Universidade Federal de Pelotas Disciplina de Genmica Prof























- Slides: 44

Universidade Federal de Pelotas Disciplina de Genômica Prof. Sibele Borsuk REP-PCR, INVERSE-PCR e VECTORETTE-PCR Delva Leão Emily Nunes Gabriela Debom Jessica Plaça Lucas Goedert 03/12/2010

Por que utilizar um PCR diferente ?

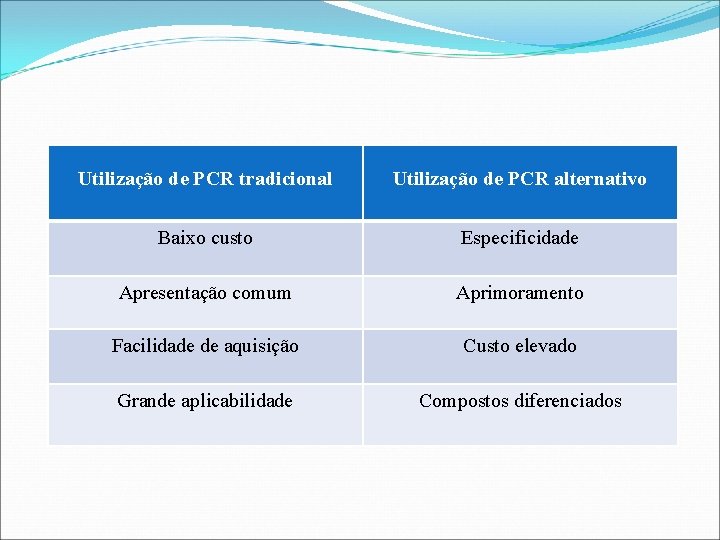
Utilização de PCR tradicional Utilização de PCR alternativo Baixo custo Especificidade Apresentação comum Aprimoramento Facilidade de aquisição Custo elevado Grande aplicabilidade Compostos diferenciados

REP-PCR (Repetitive sequence-based PCR) Método que se utiliza da presença de sequências repetitivas não-codificadoras conservadas; dispostas, aleatoriamente, no genoma.

REP-PCR Importância na identificação de sub-espécies Identificação dos fragmentos amplificados; Comparação entre os fragmentos; Processamento dos dados. Biblioteca genômica

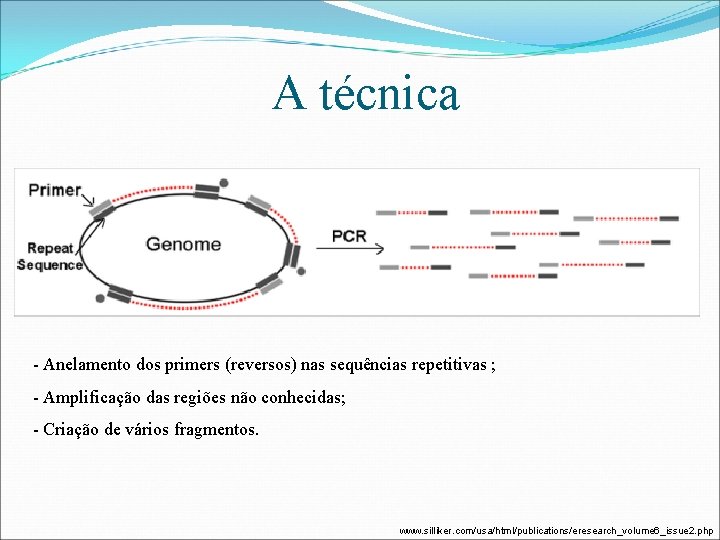
A técnica - Anelamento dos primers (reversos) nas sequências repetitivas ; - Amplificação das regiões não conhecidas; - Criação de vários fragmentos. www. silliker. com/usa/html/publications/eresearch_volume 6_issue 2. php

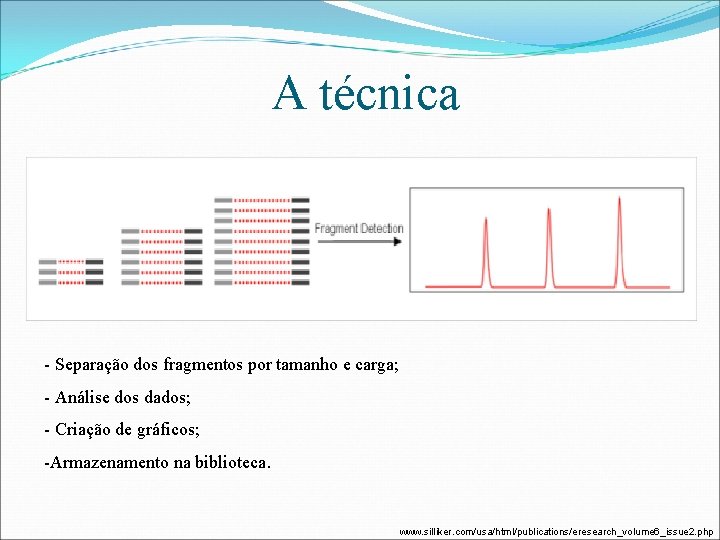
A técnica - Separação dos fragmentos por tamanho e carga; - Análise dos dados; - Criação de gráficos; -Armazenamento na biblioteca. www. silliker. com/usa/html/publications/eresearch_volume 6_issue 2. php

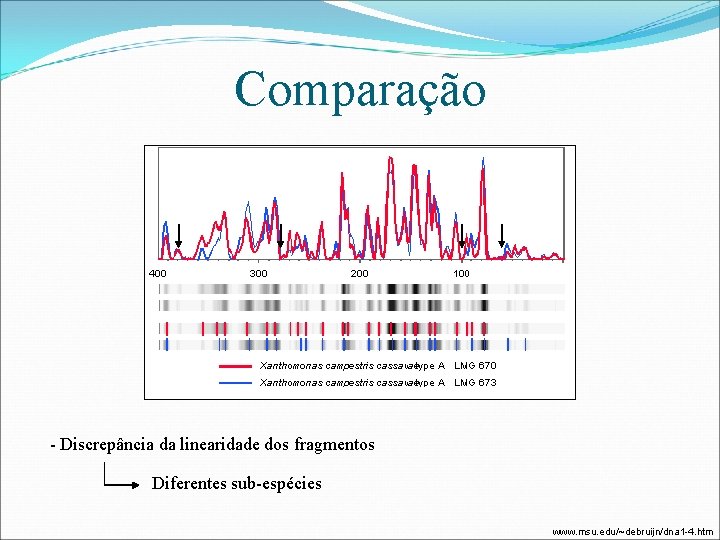
Comparação - Discrepância da linearidade dos fragmentos Diferentes sub-espécies www. msu. edu/~debruijn/dna 1 -4. htm

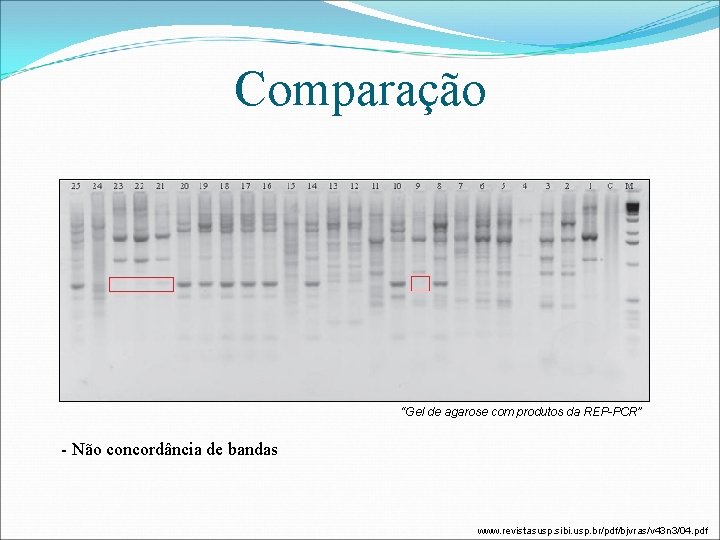
Comparação “Gel de agarose com produtos da REP-PCR” - Não concordância de bandas www. revistasusp. sibi. usp. br/pdf/bjvras/v 43 n 3/04. pdf

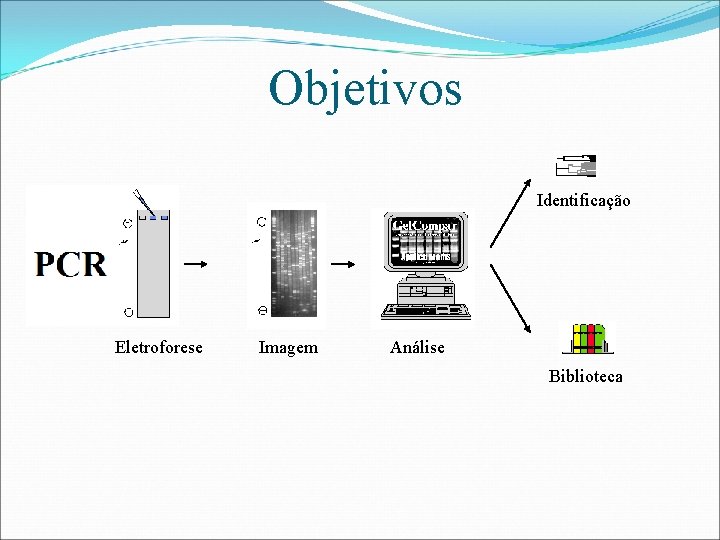
Objetivos Identificação Eletroforese Imagem Análise Biblioteca

Tipos de REP-PCR REP ( Repetitive extragenic palindromic); ERIC (Enterobacterial Repetitive Intergenic Consensus elements); BOX

REP-PCR ( Repetitive extragenic palindromic) • Unidades palindrômicas; • Apresentam de 35 – 40 pares de base; • Primer: 5´-CCGCCGTTGCCGCCG-3´

ERIC-PCR (Enterobacterial Repetitive Intergenic Consensus elements) Estruturas palindrômicas centrais Apresenta de 124 - 127 pares de base Primer: 5´-ATGTAAGCTCCTGGGGATTCAC-3´

BOX-PCR Diferentes regiões repetitivas BOX A: 5´-CTACGGCAAGGCGACGCTGACG-3 BOX B: 5´-TTCGTCAGTTCTACAACC-3´ BOX C: 5´-TGCGGCTAGCTTCCTAGTTTGC-3´

Eficiência www. msu. edu/~debruijn/dna 1 -4. htm

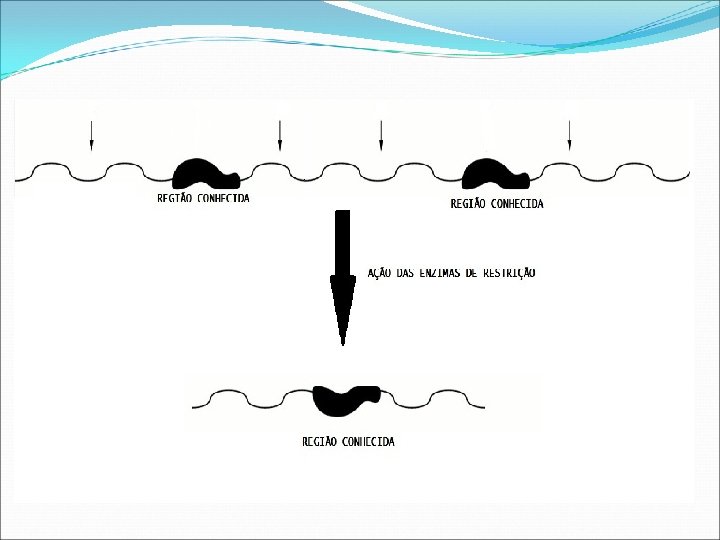
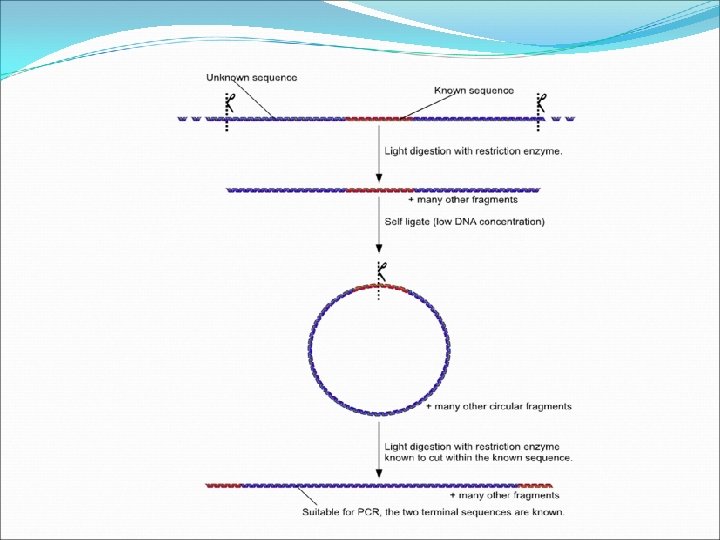
Inverse PCR Método utilizado para amplificar sequência desconhecida a partir de uma sequência conhecida.

Inverse PCR Desenvolvido por Ochman -1988 Amplificar regiões desconhecidas (4 kb) Localizadas na região upstream e downstream da região conhecida É necessário que as regiões de flanqueamento sejam conhecidas e que existam sítios de restrição. Determinar sítios de inserção, por exemplo em retrovírus e transposons que aleatoriamente integram o DNA.


Escolha das enzimas de restrição: 1. Tentativa e erro. 2. Clivagens sucessivas por enzimas de restrição que reconhecem a mesma sequência de DNA. 3. Digestão do modelo de DNA com enzimas de restrição e posterior hibridização para verificar se a enzima de restrição utilizada não digere a sequência conhecida.

Primers As sequências conhecidas são usadas para criar um primer inverso, que vai na direção oposta a um primer do PCR padrão, mas ainda hidrizida com o DNA Esses primers amplificam para fora e para longe um do outro, ao invés de para o interior em direção um ao outro.

Passos básicos 1. Isolamento do DNA molde seguido por digestão usando enzimas apropriadas (clivam as regiões upstream e downstream das regiões conhecidas) 2. Remoção dos fragmentos de restrição pra remover qualquer enzima inibitória e tampão 3. Ligação e circularização dos fragmentos de DNA usando DNA ligase 4. Amplificação usando primers inversos específicos.

Depois da digestão os vários fragmentos são ligados, uma dessas ligações será um fragmento circularizado contendo a região de interesse.

Uma enzima irá clivar a região conhecida e o DNA irá se linearizar, fazendo com que a região conhecida esteja na região upstream e downstream da região desconhecida. A região conhecida será usada como primer inverso para a atuação da DNA polimerase. Após a amplificação sequenciamento. se dá uma limpeza e o



Vectorette PCR Usado quando se conhece apenas a sequência nucleotídica de um primer.

Utilidades Genomic Walking: método de isolamento de sequências genômicas de acompanhamento (ex. regiões promotoras) adjacentes a uma sequência conhecida. Sequenciamento de insertos terminais YAC (Yeast Artificial Chromossome) e BAC (Bacterial Artificial Chromossome); Mapeamento de íntrons do DNA apartir de clones de c. DNA; Reconhecimento de regiões homólogas em diferentes genomas; Mapeamento e seqüenciamento de regiões contendo deleções, inserções, translocações.

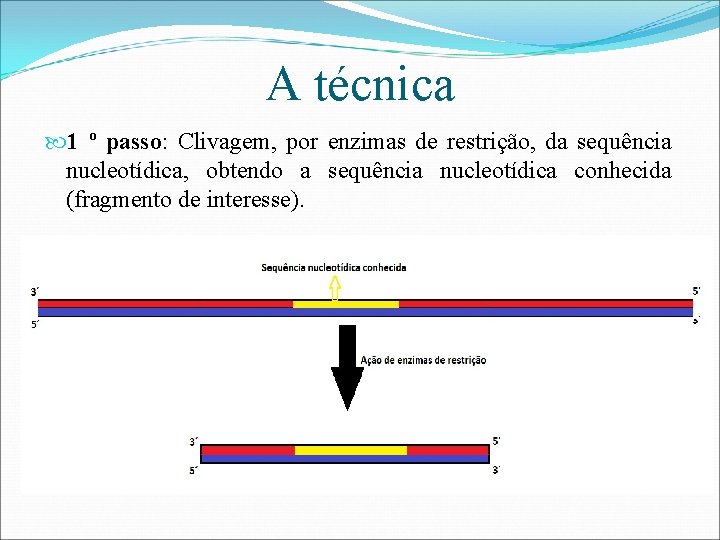
A técnica 1 º passo: Clivagem, por enzimas de restrição, da sequência nucleotídica, obtendo a sequência nucleotídica conhecida (fragmento de interesse).

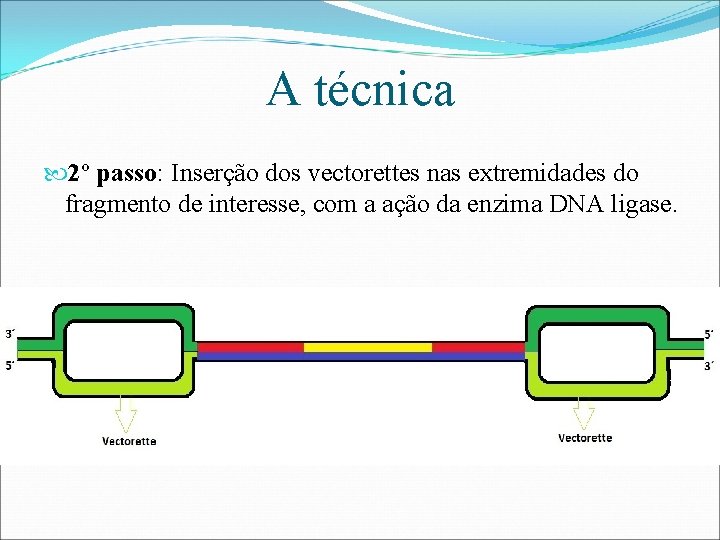
A técnica 2º passo: Inserção dos vectorettes nas extremidades do fragmento de interesse, com a ação da enzima DNA ligase.

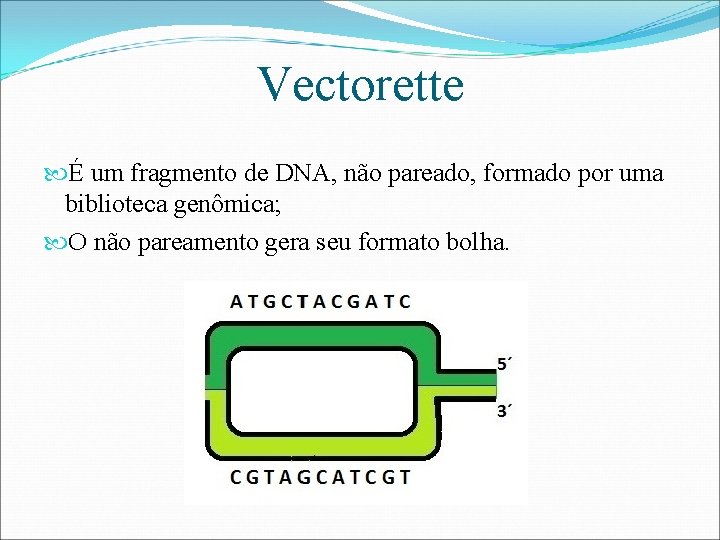
Vectorette É um fragmento de DNA, não pareado, formado por uma biblioteca genômica; O não pareamento gera seu formato bolha.

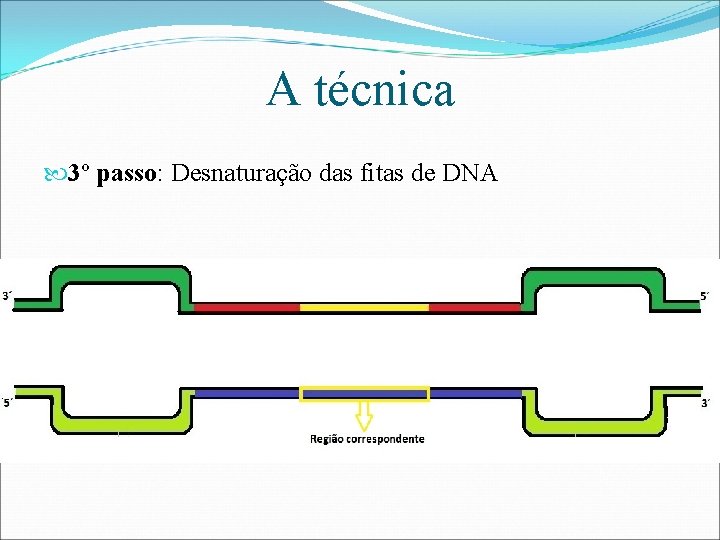
A técnica 3º passo: Desnaturação das fitas de DNA

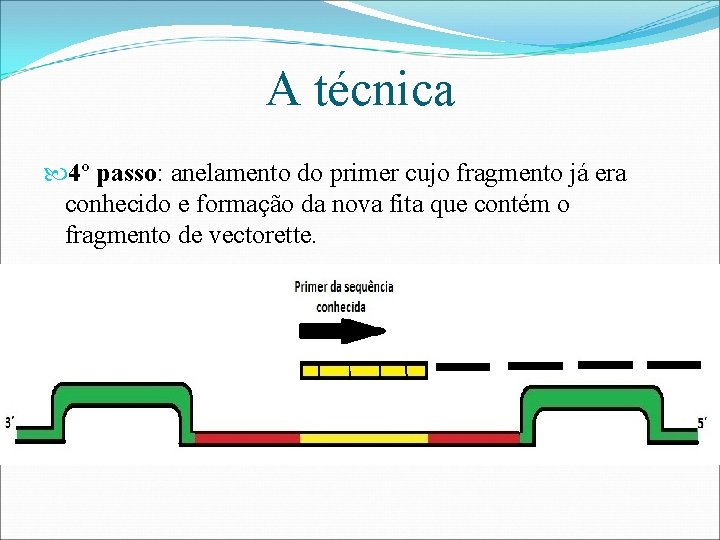
A técnica 4º passo: anelamento do primer cujo fragmento já era conhecido e formação da nova fita que contém o fragmento de vectorette.

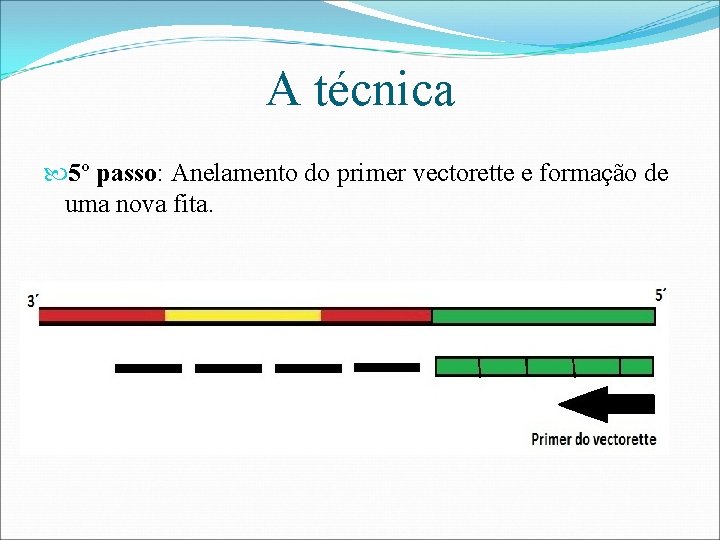
A técnica 5º passo: Anelamento do primer vectorette e formação de uma nova fita.

A técnica É importante ressaltar : O processo de anelamento de primers ocorre duas vezes, já que o DNA é constituído de fita dupla; O vectorette é fator essencial na ocorrência do PCR, e seu primer se encontra na fita inferior da região não-pareada; Só ocorre a amplificação dos vectorettes se estiverem ligados ao DNA de interesse; O anelamento do primer que era anteriormente conhecido sempre ocorrerá primeiro;

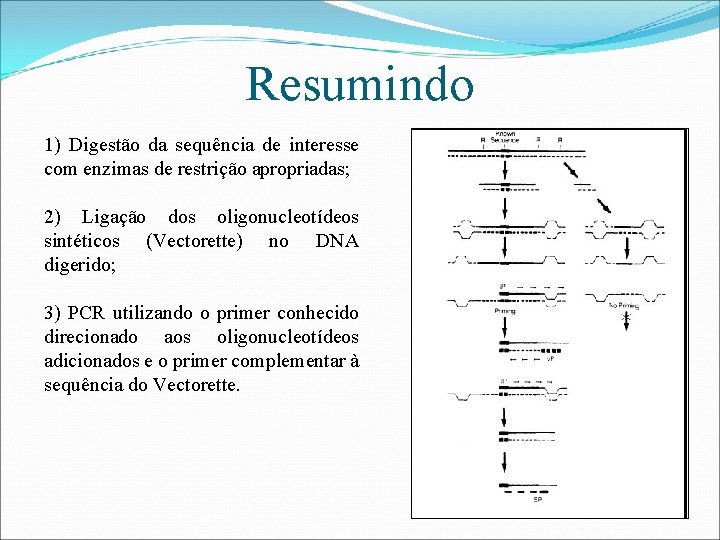
Resumindo 1) Digestão da sequência de interesse com enzimas de restrição apropriadas; 2) Ligação dos oligonucleotídeos sintéticos (Vectorette) no DNA digerido; 3) PCR utilizando o primer conhecido direcionado aos oligonucleotídeos adicionados e o primer complementar à sequência do Vectorette.

Protocolo • Digestão do DNA com enzimas de restrição e tampão apropriado (37°C 1 h); • Ligação do DNA de interesse com a unidade de Vectorette através de DNA -Ligase T 4, ATP (2 m. M) e dithiothereitol (DTT) (2 m. M); • Detalhe importante: Não há necessidade de troca de tampão. Enquanto são digeridas as ligações DNA-DNA, são formadas novas ligações DNAVectorette, e essas novas ligações formadas não são digeridas pelas enzimas de restrição;

Protocolo Incubação das amostras a 20°C por 1 h, seguido de 37°C por 30 min. Feito duas vezes para garantir o processo; PCR utilizando o primer previamente conhecido e o primer de Vectorette. Adição do tampão 1 x, Taq polimerase, d. NTPs e Mg. Cl 2; Ajustar o termociclador para 40 ciclos de 96°C por 1 min, 64°C por min e 74°C 1, 5 min; Visualização das amostras através de eletroforese em gel de agarose 1%.

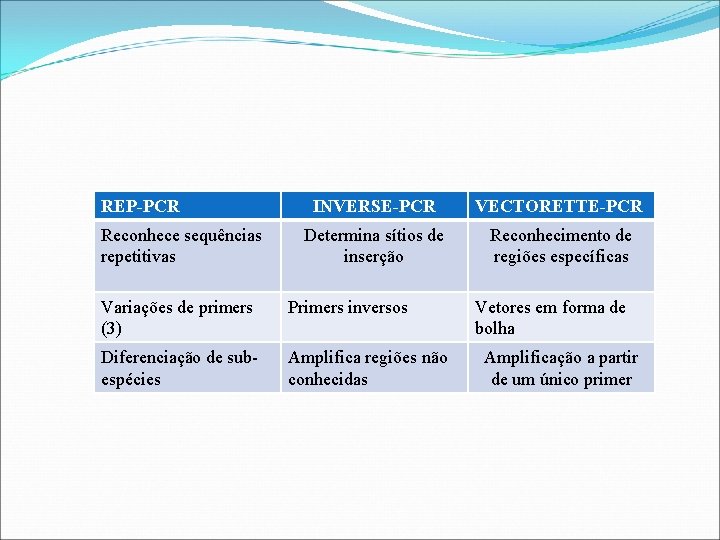
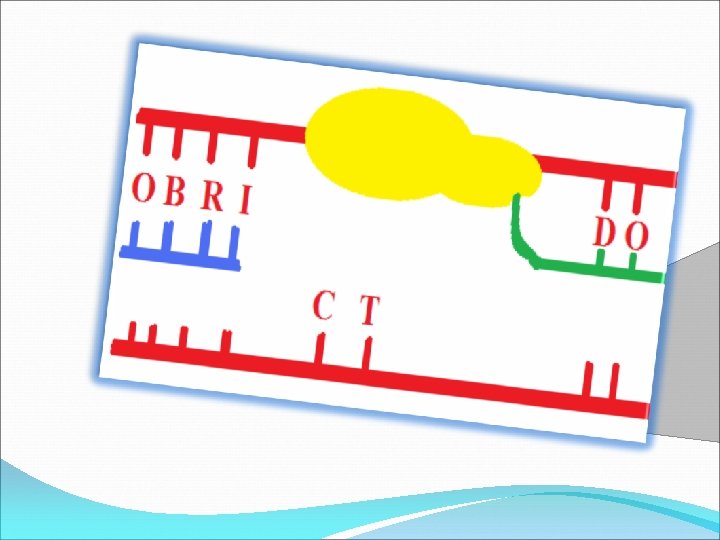
REP-PCR Reconhece sequências repetitivas INVERSE-PCR VECTORETTE-PCR Determina sítios de inserção Reconhecimento de regiões específicas Variações de primers (3) Primers inversos Diferenciação de subespécies Amplifica regiões não conhecidas Vetores em forma de bolha Amplificação a partir de um único primer

Utilização em Pesquisa Números Pub. Med http: //www. ncbi. nlm. nih. gov/pubmed/

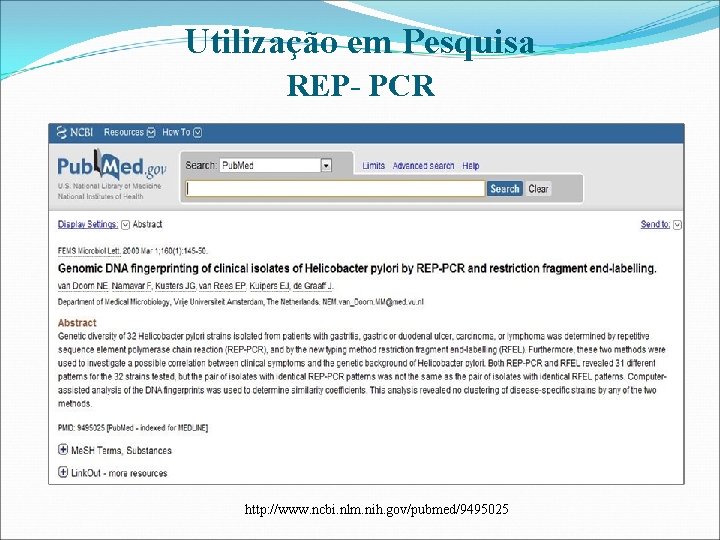
Utilização em Pesquisa REP- PCR http: //www. ncbi. nlm. nih. gov/pubmed/9495025

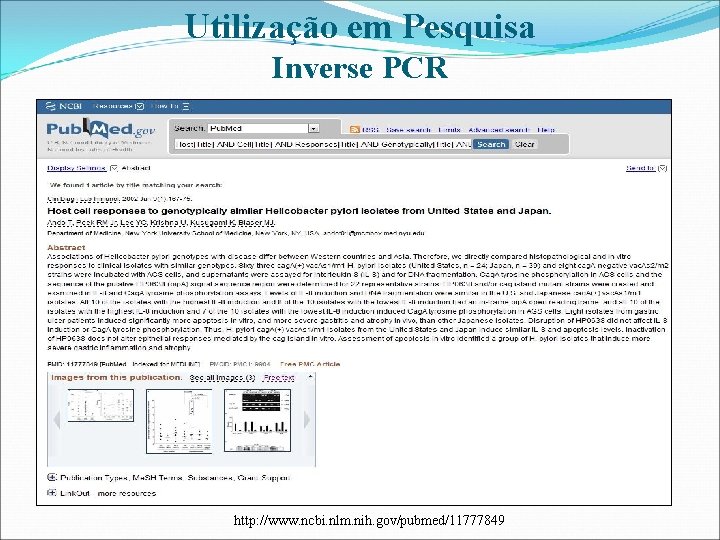
Utilização em Pesquisa Inverse PCR http: //www. ncbi. nlm. nih. gov/pubmed/11777849

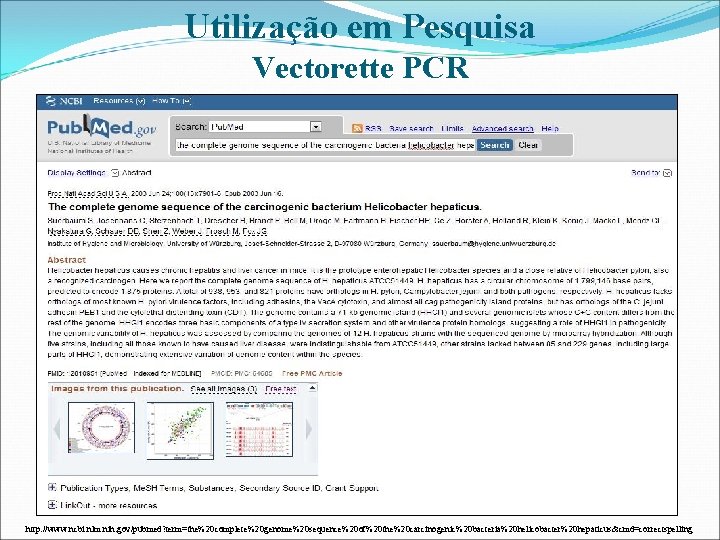
Utilização em Pesquisa Vectorette PCR http: //www. ncbi. nlm. nih. gov/pubmed? term=the%20 complete%20 genome%20 sequence%20 of%20 the%20 carcinogenic%20 bacteria%20 helicobacter%20 hepaticus&cmd=correctspelling

Artigos Bibliografia ARNOLD C. , HODGSON, I. J. Vectorette PCR: a novel approach to genomic walking. Genome Res. 1991 1: 39 -42 DAVID, K. ; AKASHI. A Vectorette PCR-based approach for sequencing homologous regions from different genomes. Hiroshi Akashi Lab Biology Department Pennsylvania State University. OCHMAN, H, GERBER A. S. , HARTL DL. Genetic applications of an inverse polymerase chain reaction. Genetics. 1988; 120: 621– 623 Sites Evrogen. Genome walking. Disponível em: <http: //www. evrogen. com/technologies/genome-walking. shtml>. Acesso em 1 dez. 2010. Microbe Inotech , Inc. Repetitive Sequence-based PCR (rep. PCR). Disponível em: <http: //www. microbeindustrial. com/services/reppcr>. Acesso em 1 dez. 2010. Biomerieux. Aplicações Bio-Farmacêuticas. Disponível em: <http: //www. biomerieux. com. br/servlet/srt/bio/brazil/dyn. Page? open=BRZ_IND_BPA_PRD&doc=BRZ_IND_BPA_ PRD_G_PRD_NDY_4&pubparams. sform=5&lang=pt_br>. Acesso em 1 dez. 2010. Silliker. Microbial Identification: Tracking the Great Unknown with Innovative and Advanced Technologies. Disponível em: <http: //www. silliker. com/usa/html/publications/eresearch_volume 6_issue 2. php>. Acesso em 1 dez. 2010. Michigan State University. Characterization and classification of microbes by rep- pcr genomic fingerprinting and computer-assisted pattern analysis. Disponível em: <https: //www. msu. edu/~debruijn/dna 1 -4. htm>. Acesso em 1 dez. 2010. Annual reviews. The three DS of PCR-based genomic analysis of phytobacteria: Diversity, Detection, and Disease Diagnosis. Disponível em: <http: //www. annualreviews. org/doi/full/10. 1146/annurev. phyto. 37. 1. 81>. Acesso em 1 dez. 2010. Clinical lab products. Rep-PCR technology speeds shift to DNA fingerprintingrep-PCR technology speeds shift to DNA fingerprinting. Disponível em: <http: //www. clpmag. com/issues/articles/2003 -05_04. asp>. Acesso em 1 dez. 2010.
