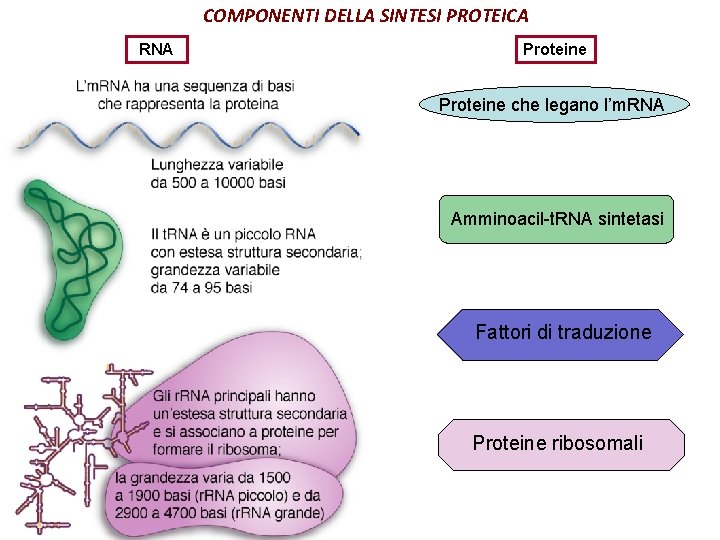
COMPONENTI DELLA SINTESI PROTEICA RNA Proteine che legano










- Slides: 41

COMPONENTI DELLA SINTESI PROTEICA RNA Proteine che legano l’m. RNA Amminoacil-t. RNA sintetasi Fattori di traduzione Proteine ribosomali

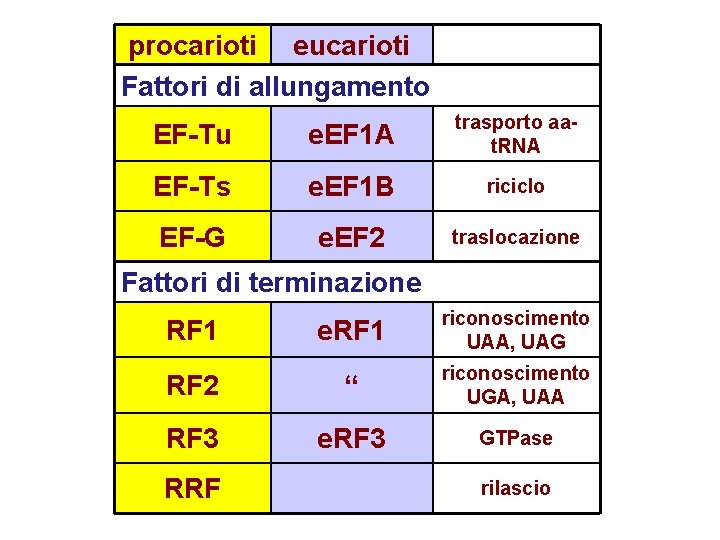
procarioti eucarioti Fattori di allungamento EF-Tu e. EF 1 A trasporto aat. RNA EF-Ts e. EF 1 B riciclo EF-G e. EF 2 traslocazione Fattori di terminazione RF 1 e. RF 1 riconoscimento UAA, UAG RF 2 “ riconoscimento UGA, UAA RF 3 e. RF 3 GTPase RRF rilascio

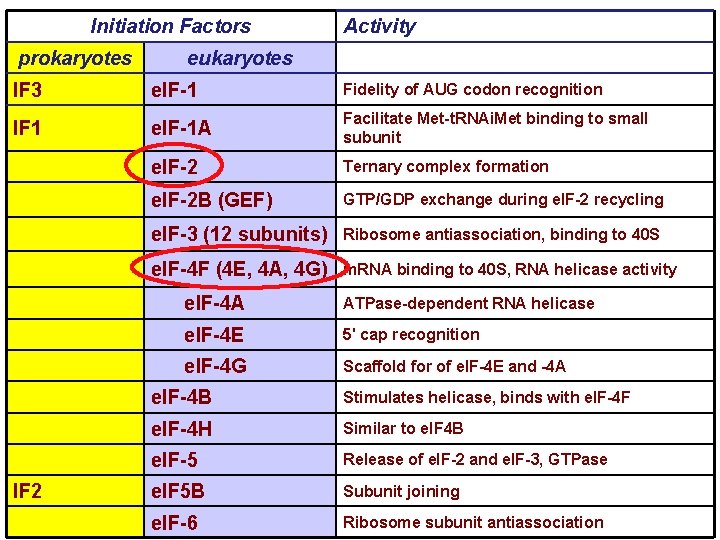
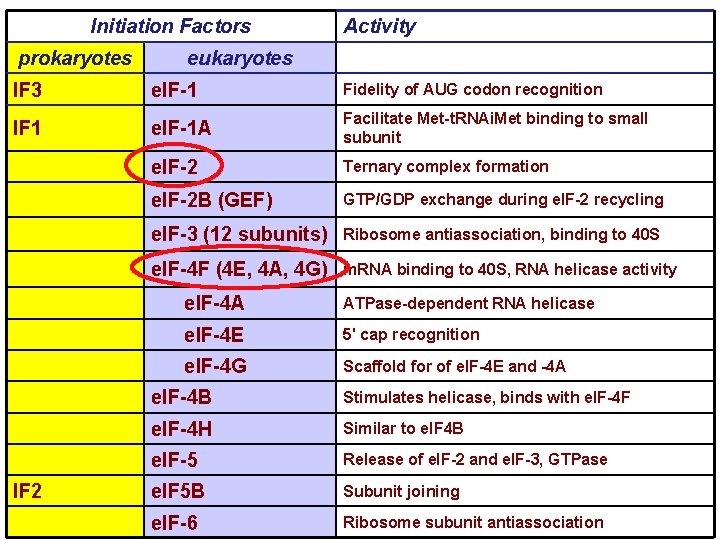
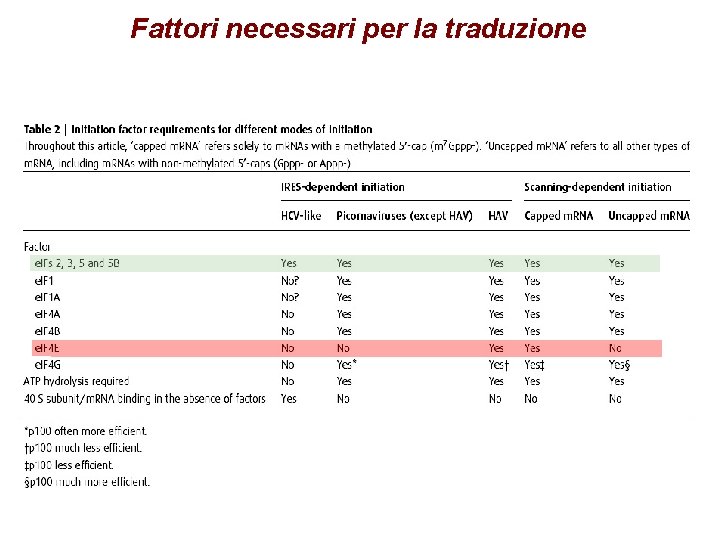
Initiation Factors prokaryotes Activity eukaryotes IF 3 e. IF-1 Fidelity of AUG codon recognition IF 1 e. IF-1 A Facilitate Met-t. RNAi. Met binding to small subunit e. IF-2 Ternary complex formation e. IF-2 B (GEF) GTP/GDP exchange during e. IF-2 recycling e. IF-3 (12 subunits) Ribosome antiassociation, binding to 40 S e. IF-4 F (4 E, 4 A, 4 G) m. RNA binding to 40 S, RNA helicase activity IF 2 e. IF-4 A ATPase-dependent RNA helicase e. IF-4 E 5' cap recognition e. IF-4 G Scaffold for of e. IF-4 E and -4 A e. IF-4 B Stimulates helicase, binds with e. IF-4 F e. IF-4 H Similar to e. IF 4 B e. IF-5 Release of e. IF-2 and e. IF-3, GTPase e. IF 5 B Subunit joining e. IF-6 Ribosome subunit antiassociation


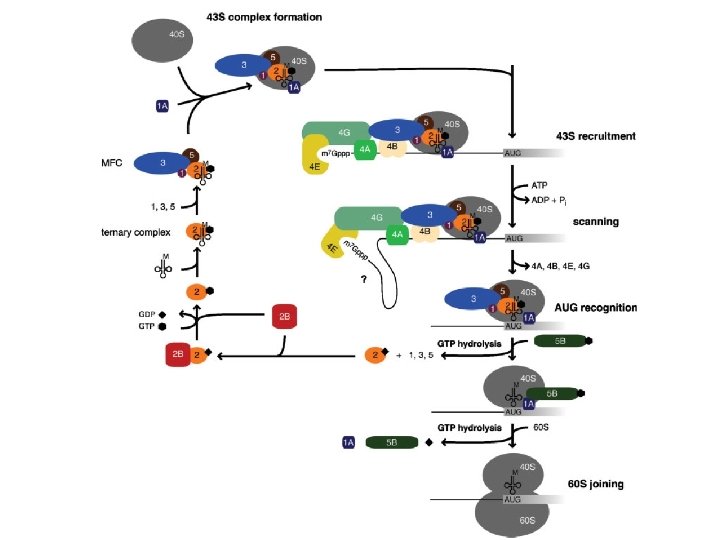
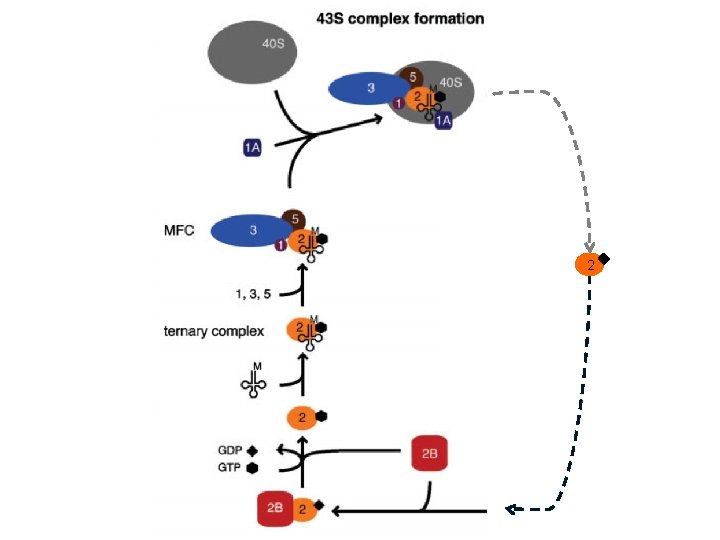
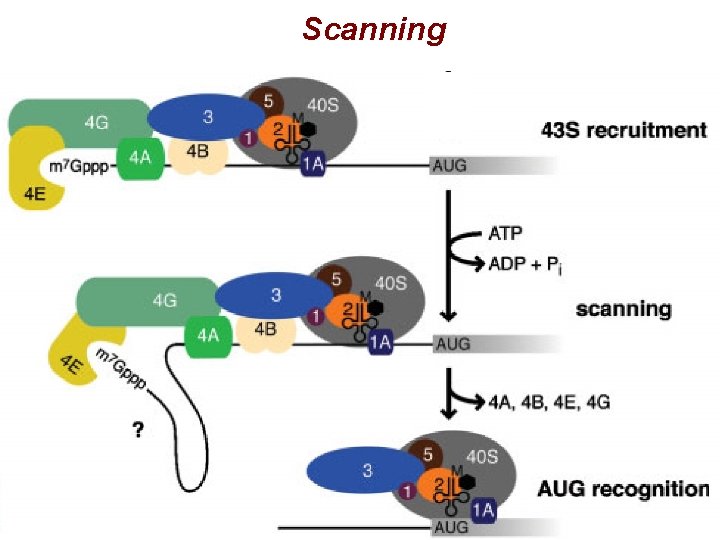
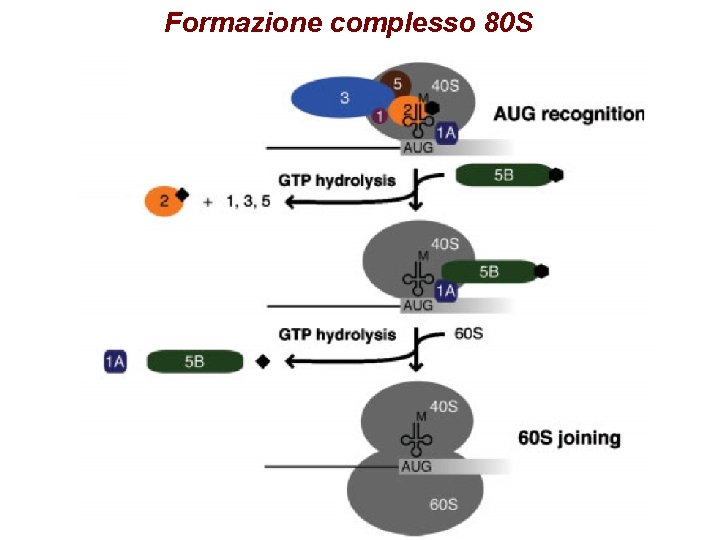
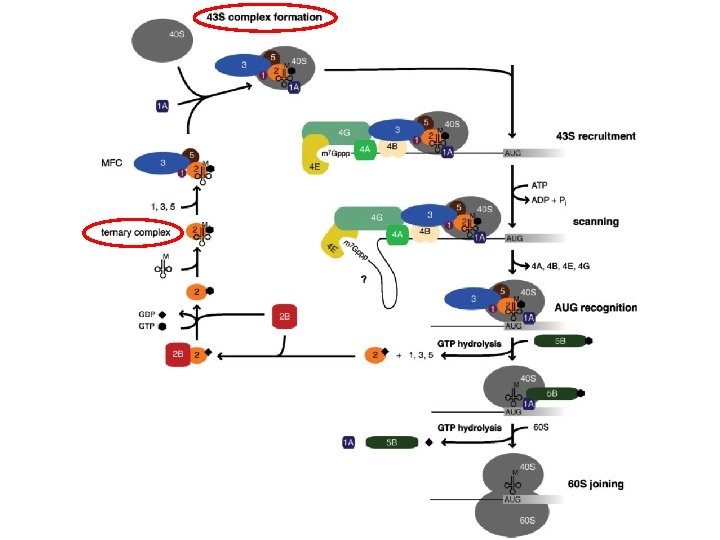
Passaggi dell’inizio di traduzione 1. Formazione complesso 43 S 2. Reclutamento del complesso 43 S sul 5’ dell’m. RNA (48 S) 3. Scanning del 5’ UTR e riconoscimento dell’AUG 4. Formazione del complesso 80 S

2

e. IF 2 § 3 subunità: a, b, g § Subunità b aiuta attività di GTPasi e modula il legame t. RNAi-e. IF 2 g § Subunità a è un regolatore della traduzione. E’ fosforilata (ser 51) da diverse chinasi in risposta a stress e. IF 2 B § 5 subunità: a, b, g, d, e § Fattore di scambio GDP-GTP (GEF) per e. IF 2 § 2 subcomplessi: d, e attività catalitica a, b, g attività regolativa

e. IF 3 § 10 -11 subunità § Nucleo di 5 subunità: e. IF 3 a, b, c, i, g § In lievito forma un complesso con e. IF 1, e. IF 2, e. IF 5, Met-t. RNAi (MFC) § Richiesto per il legame del 43 S all’m. RNA

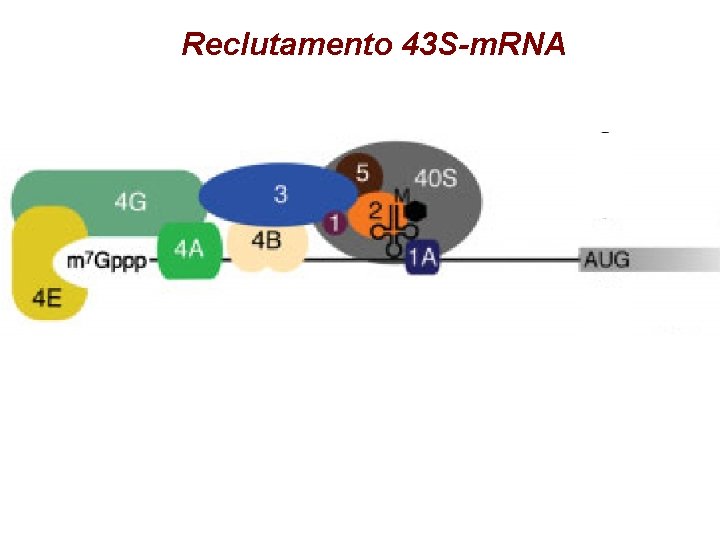
Reclutamento 43 S-m. RNA

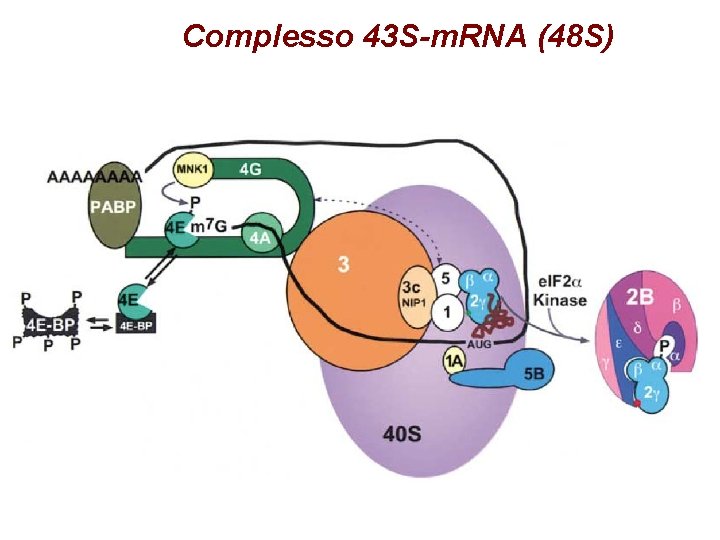
Complesso 43 S-m. RNA (48 S)

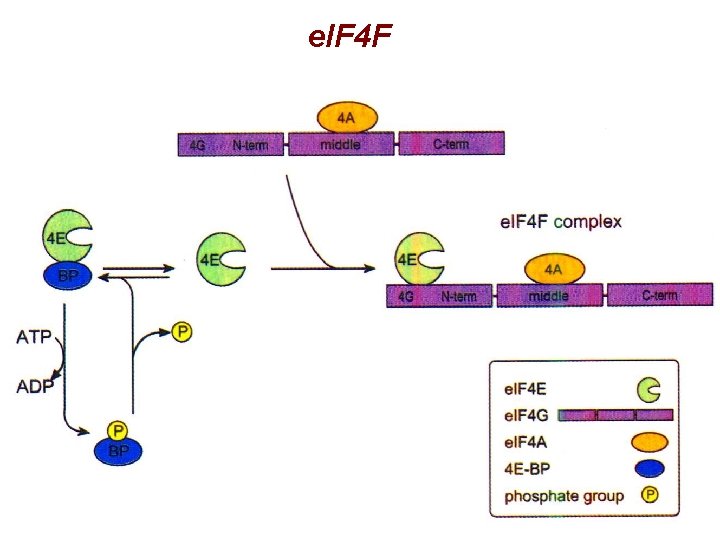
e. IF 4 F

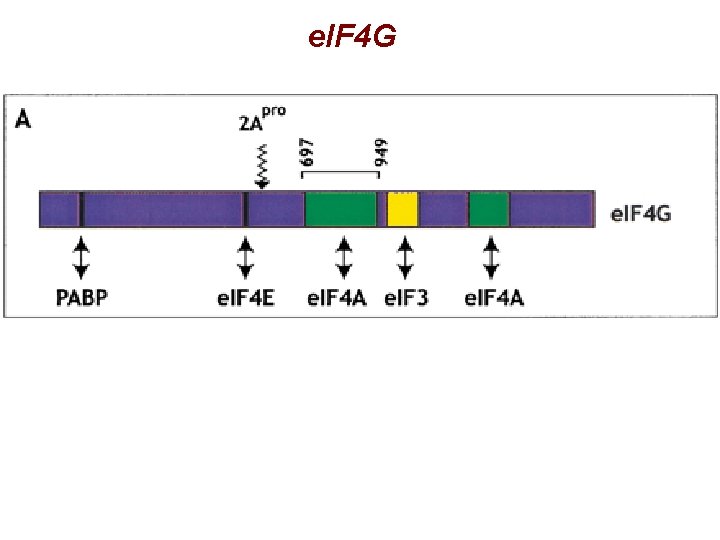
e. IF 4 F § Composto da 3 subunità e. IF 4 A: elicasi, aiutato da e. IF 4 B e. IF 4 E: cap binding protein, regolato da fosforilazione e interazione con e. IF 4 E-BP e. IF 4 G: adattatore, interagisce con diversi fattori

e. IF 4 G

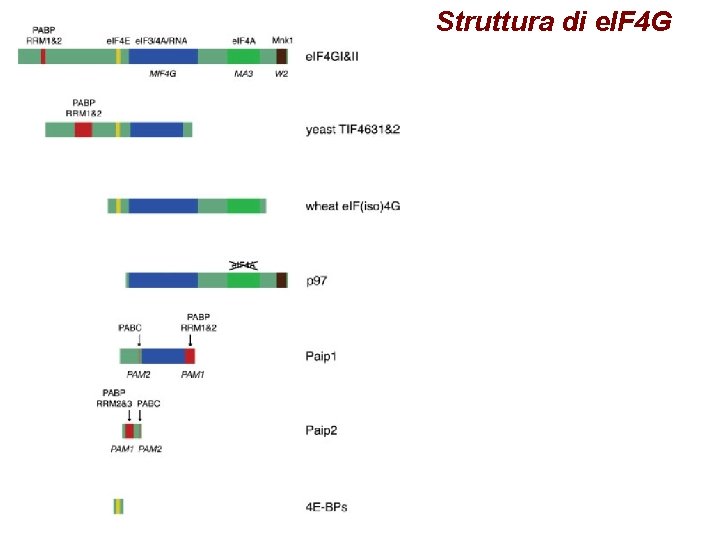
Struttura di e. IF 4 G

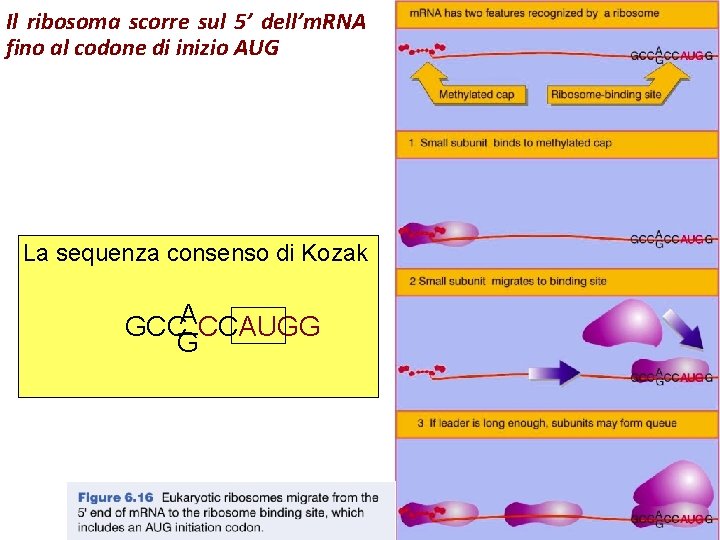
Il ribosoma scorre sul 5’ dell’m. RNA fino al codone di inizio AUG La sequenza consenso di Kozak A _ GCC CCAUGG G

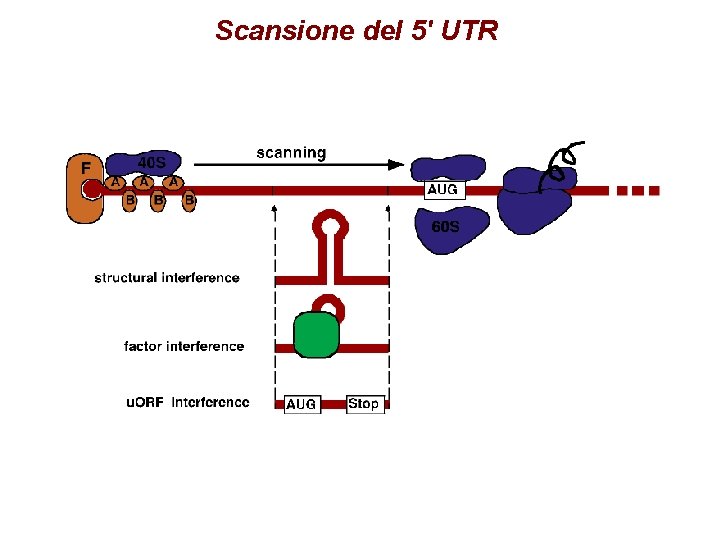
Scansione del 5' UTR

Scanning

Formazione complesso 80 S

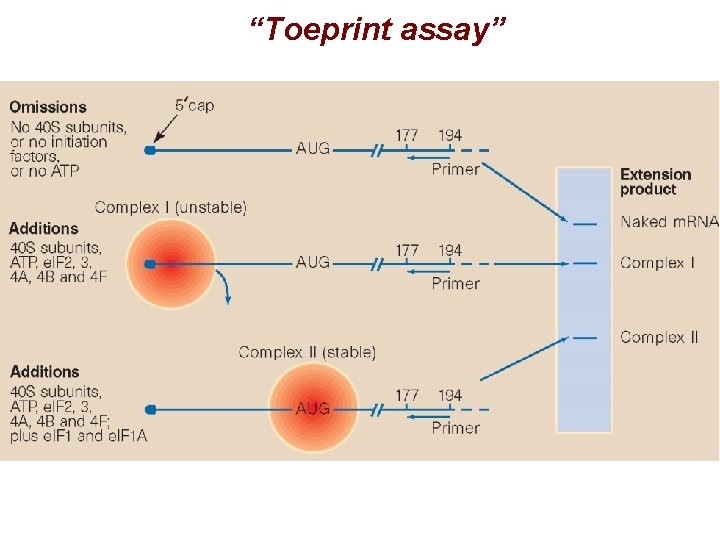
“Toeprint assay”

Scanning § 40 S, ATP, e. IF 2, e. IF 4 A, e. IF 4 B, e. IF 4 F, m. RNA sufficienti per formare complesso I (non produttivo) § e. IF 1, e. IF 1 A necessari per il complesso II (scanning fino all’AUG) § Se non ci sono strutture secondarie e. IF 4 A, 4 B, 4 F non sono necessari (in vitro)

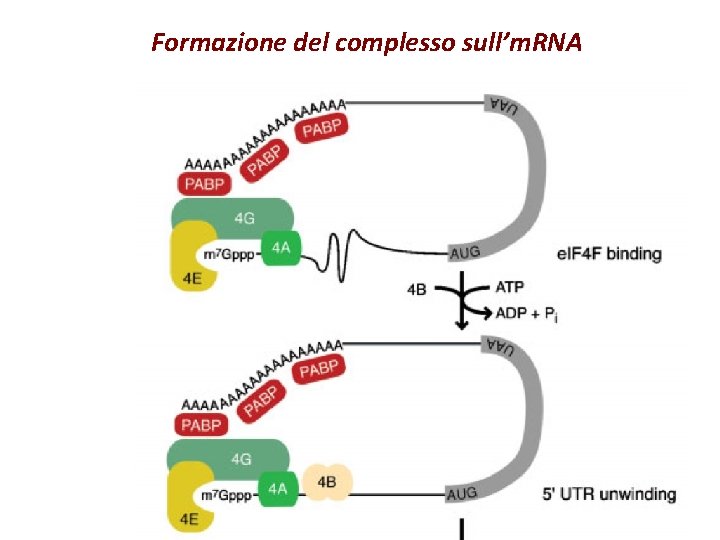
Formazione del complesso sull’m. RNA

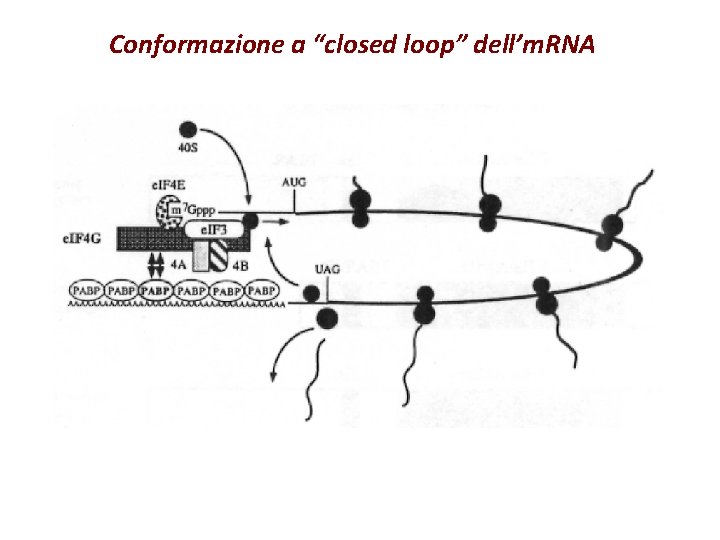
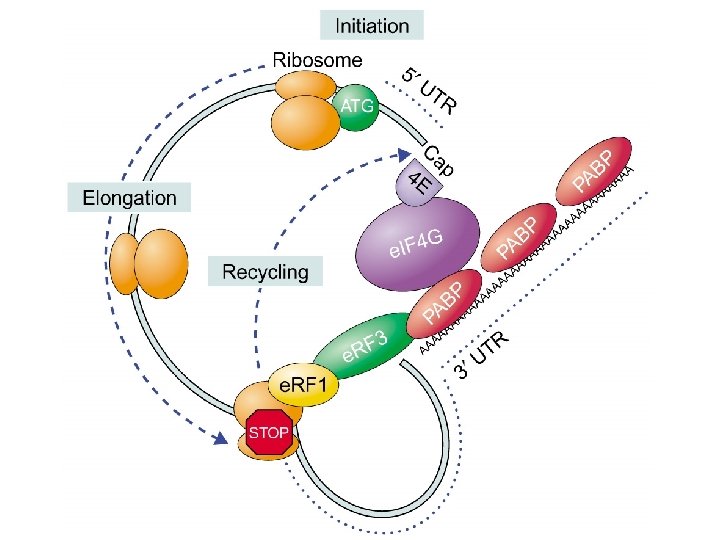
Conformazione a “closed loop” dell’m. RNA


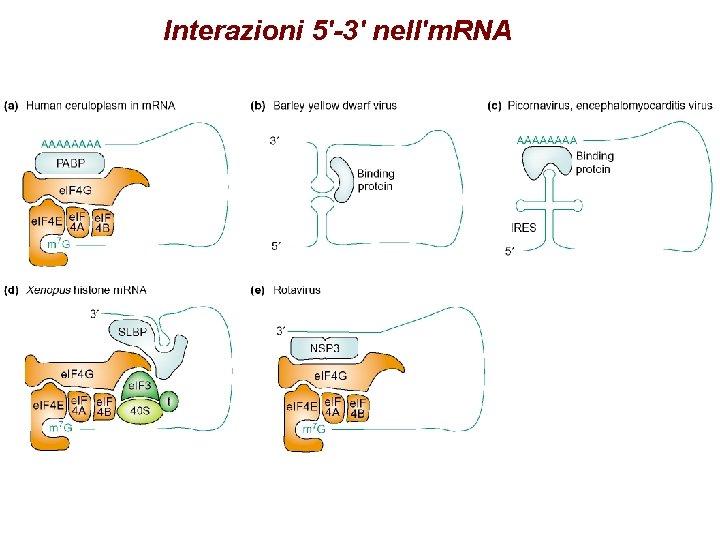
Interazioni 5'-3' nell'm. RNA

Ruolo di PABP nella traduzione § In estratti “cell free” di lievito sinergismo tra cap e coda poli(A) § Interazione tra PABP e e. IF 4 G § e. IF 4 E, e. IF 4 G, PABP e m. RNA formano strutture circolari (in vitro) § Altre proteine che interagiscono con PABP (Paip 1, 2 e e. RF 3)


Initiation Factors prokaryotes Activity eukaryotes IF 3 e. IF-1 Fidelity of AUG codon recognition IF 1 e. IF-1 A Facilitate Met-t. RNAi. Met binding to small subunit e. IF-2 Ternary complex formation e. IF-2 B (GEF) GTP/GDP exchange during e. IF-2 recycling e. IF-3 (12 subunits) Ribosome antiassociation, binding to 40 S e. IF-4 F (4 E, 4 A, 4 G) m. RNA binding to 40 S, RNA helicase activity IF 2 e. IF-4 A ATPase-dependent RNA helicase e. IF-4 E 5' cap recognition e. IF-4 G Scaffold for of e. IF-4 E and -4 A e. IF-4 B Stimulates helicase, binds with e. IF-4 F e. IF-4 H Similar to e. IF 4 B e. IF-5 Release of e. IF-2 and e. IF-3, GTPase e. IF 5 B Subunit joining e. IF-6 Ribosome subunit antiassociation

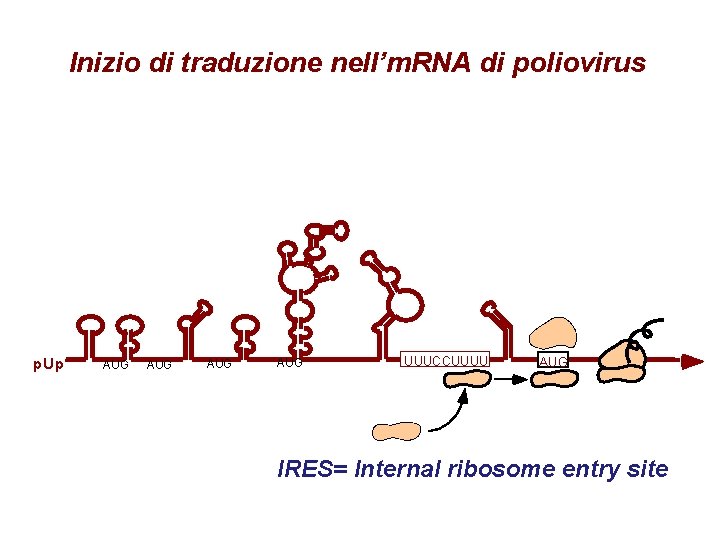
Inizio di traduzione nell’m. RNA di poliovirus p. Up AUG AUG UUUCCUUUU AUG IRES= Internal ribosome entry site

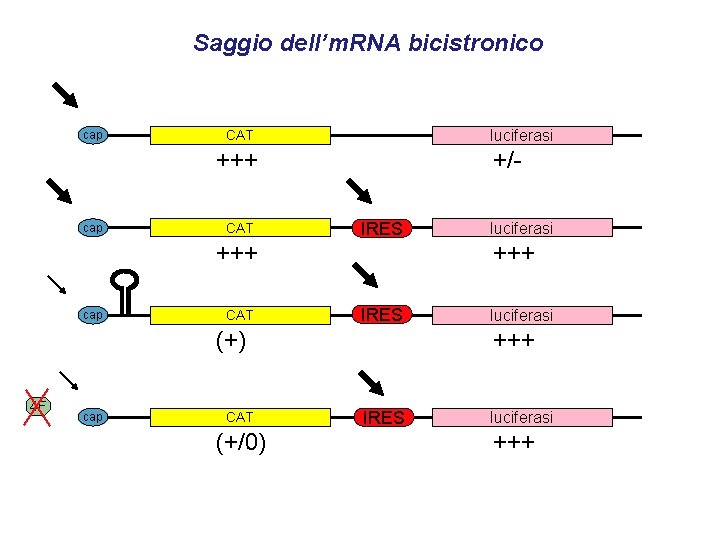
Saggio dell’m. RNA bicistronico cap luciferasi CAT +/- +++ cap CAT IRES cap CAT (+/0) luciferasi +++ (+) 4 F luciferasi IRES luciferasi +++


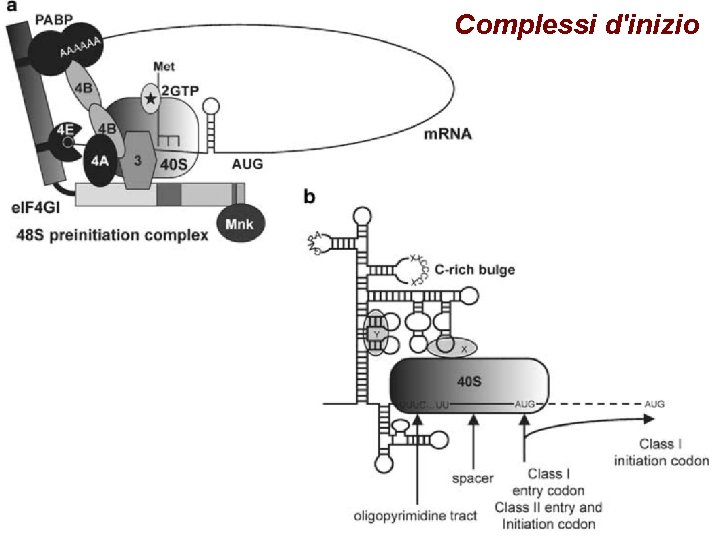
Complessi d'inizio

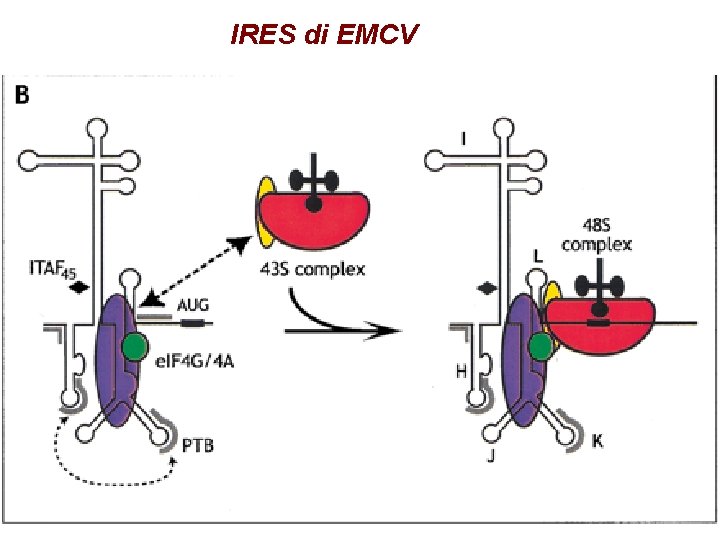
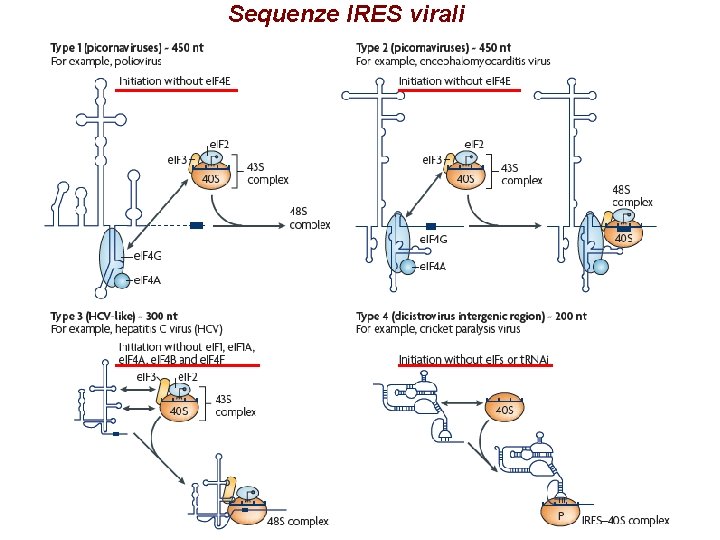
IRES di EMCV

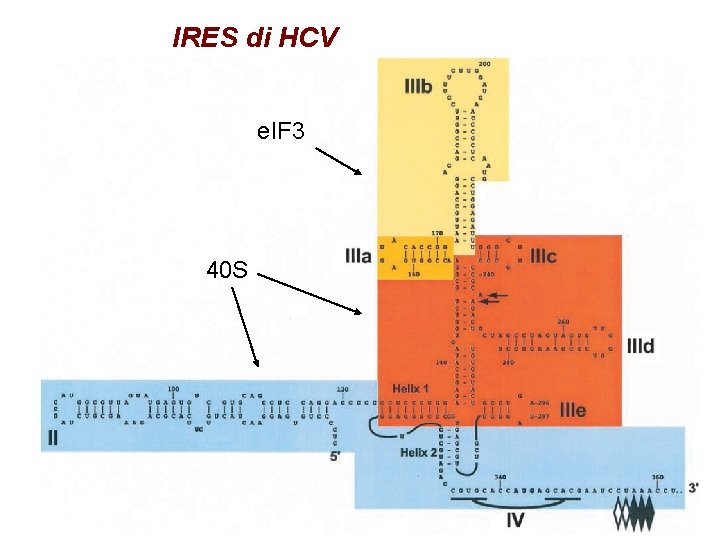
IRES di HCV e. IF 3 40 S

Fattori necessari per la traduzione

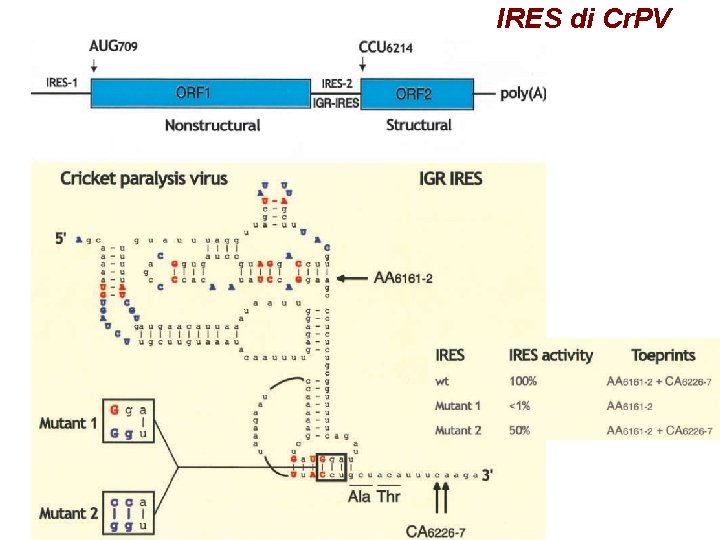
IRES di Cr. PV

Sequenze IRES virali

IRES negli m. RNA cellulari

Ruolo delle IRES

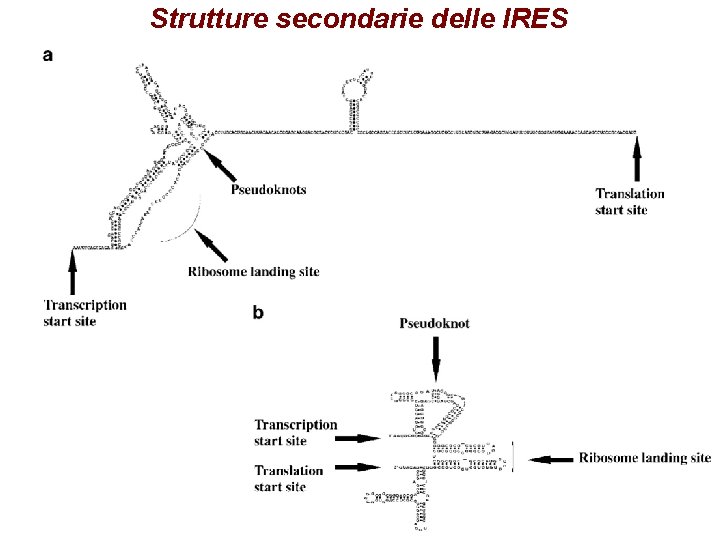
Strutture secondarie delle IRES

Fattori trans-agenti delle IRES (ITAF)

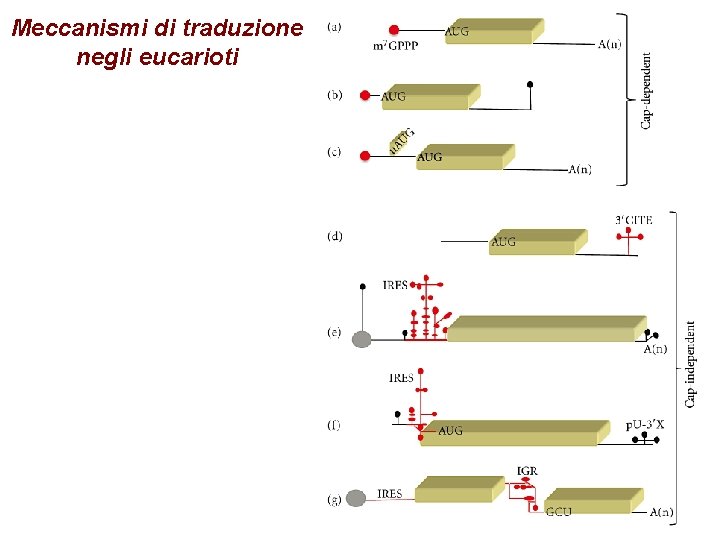
Meccanismi di traduzione negli eucarioti