TRANSCRIPCIN EN EUCARIOTAS Vernica Fernndez Mancebo 2013 TRANSCRIPCIN

TRANSCRIPCIÓN EN EUCARIOTAS Verónica Fernández Mancebo 2013

TRANSCRIPCIÓN: • Es la síntesis de una cadena de ARN • Representa a una de las hebras de ADN (hebra codificante) y es complementaria a la que le sirvió como molde
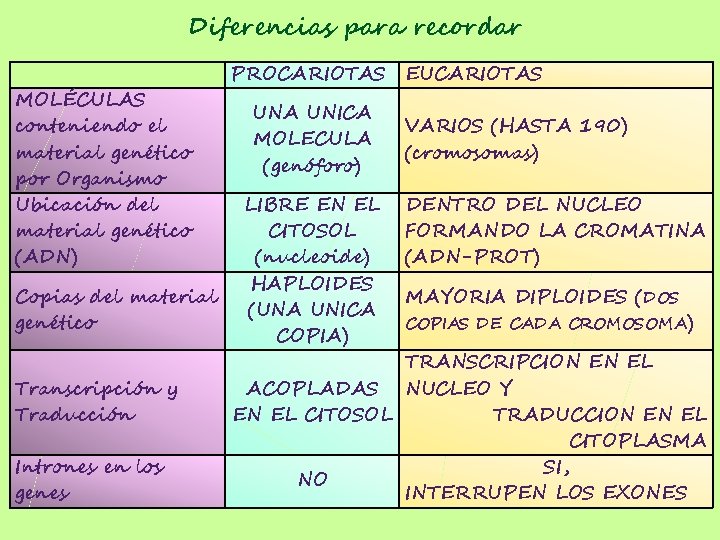
Diferencias para recordar MOLÉCULAS conteniendo el material genético por Organismo Ubicación del material genético (ADN) Copias del material genético Transcripción y Traducción Intrones en los genes PROCARIOTAS UNA UNICA MOLECULA (genóforo) LIBRE EN EL CITOSOL (nucleoide) HAPLOIDES (UNA UNICA COPIA) EUCARIOTAS VARIOS (HASTA 190) (cromosomas) DENTRO DEL NUCLEO FORMANDO LA CROMATINA (ADN-PROT) MAYORIA DIPLOIDES (DOS COPIAS DE CADA CROMOSOMA) TRANSCRIPCION EN EL ACOPLADAS NUCLEO Y EN EL CITOSOL TRADUCCION EN EL CITOPLASMA SI, NO INTERRUPEN LOS EXONES

Repasando… CROMATINA Complejo de ADN-proteínas Proteínas -> histonas (peq ricas en K y R) ->no-histonas (polimerasas, factores de transcr, etc. ) Nucleosoma Unidad estructural repetida que forma la cromatina (146 pb que envuelve un octámero de histomas)
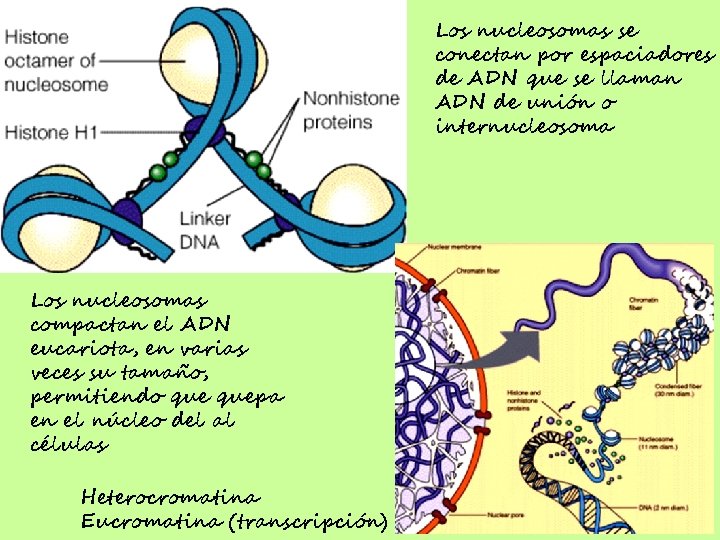
Los nucleosomas se conectan por espaciadores de ADN que se llaman ADN de unión o internucleosoma Los nucleosomas compactan el ADN eucariota, en varias veces su tamaño, permitiendo quepa en el núcleo del al células Heterocromatina Eucromatina (transcripción)

Síntesis de ARN en eucariotas: • ARN polimerasas (I, II y III) • Utiliza promotores y tiene un importante uso de “enhancers” (potenciadores) • Factores de transcripción (interaccionan con ADN y otros factores) • Poca regulación en el punto de terminación • Los ARN transcriptos primarios son ampliamente procesados
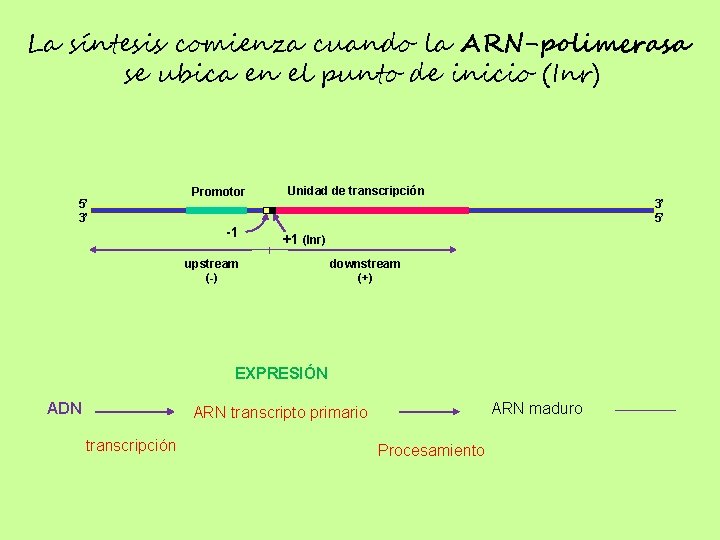
La síntesis comienza cuando la ARN-polimerasa se ubica en el punto de inicio (Inr) 5’ 3’ Promotor -1 Unidad de transcripción 3’ 5’ +1 (Inr) upstream (-) downstream (+) EXPRESIÓN ADN ARN maduro ARN transcripto primario transcripción Procesamiento
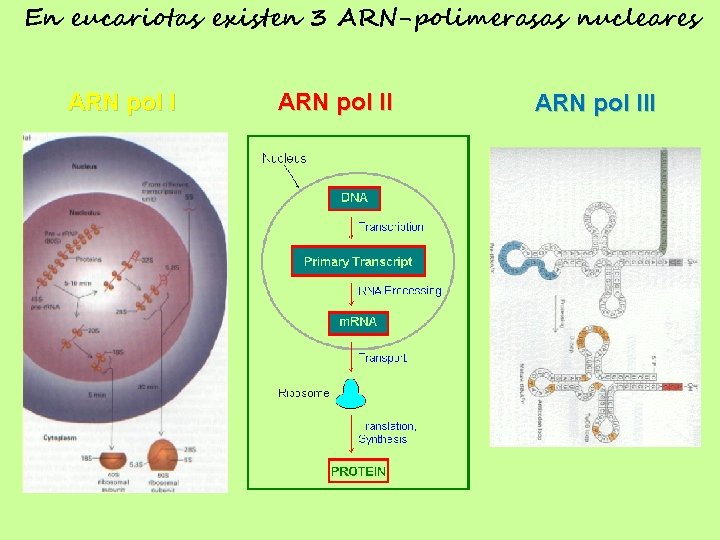
En eucariotas existen 3 ARN-polimerasas nucleares ARN pol III
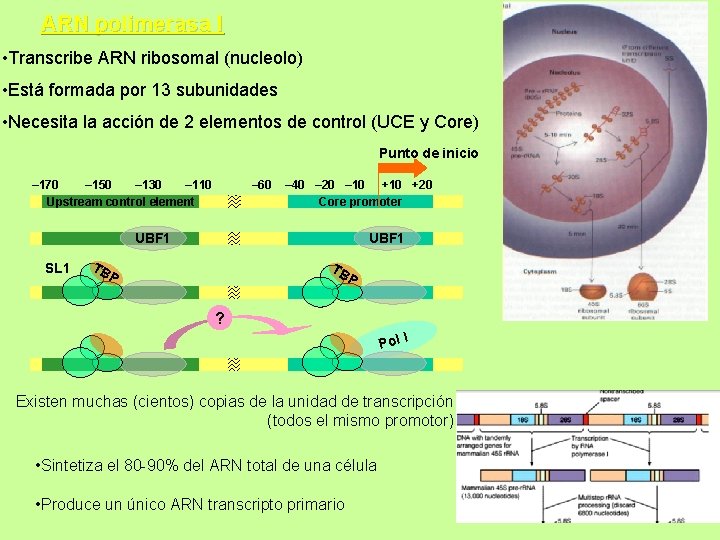
ARN polimerasa I • Transcribe ARN ribosomal (nucleolo) • Está formada por 13 subunidades • Necesita la acción de 2 elementos de control (UCE y Core) Punto de inicio – 170 – 150 – 130 – 110 Upstream control element – 60 – 40 – 20 – 10 +20 Core promoter UBF 1 SL 1 UBF 1 TB TB P P ? Pol I Existen muchas (cientos) copias de la unidad de transcripción (todos el mismo promotor) • Sintetiza el 80 -90% del ARN total de una célula • Produce un único ARN transcripto primario
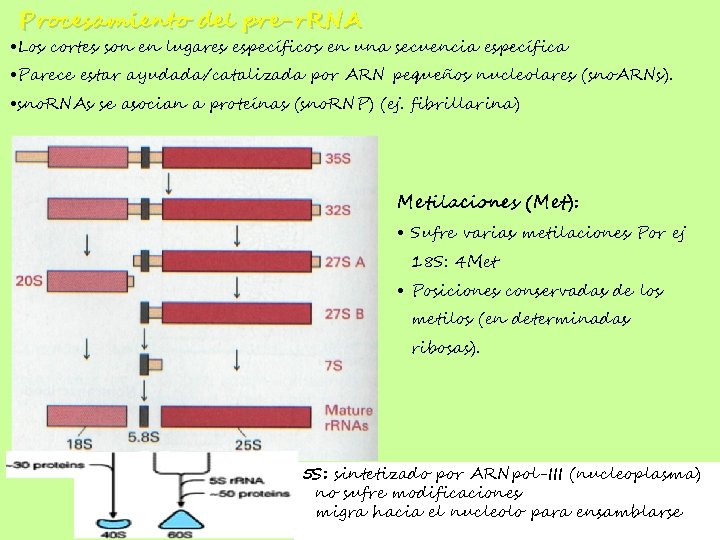
Procesamiento del pre-r. RNA • Los cortes son en lugares específicos en una secuencia específica • Parece estar ayudada/catalizada por ARN pequeños nucleolares (sno. ARNs). • sno. RNAs se asocian a proteínas (sno. RNP) (ej. fibrillarina) Metilaciones (Met): • Sufre varias metilaciones Por ej 18 S: 4 Met • Posiciones conservadas de los metilos (en determinadas ribosas). 5 S: sintetizado por ARNpol-III (nucleoplasma) no sufre modificaciones migra hacia el nucleolo para ensamblarse
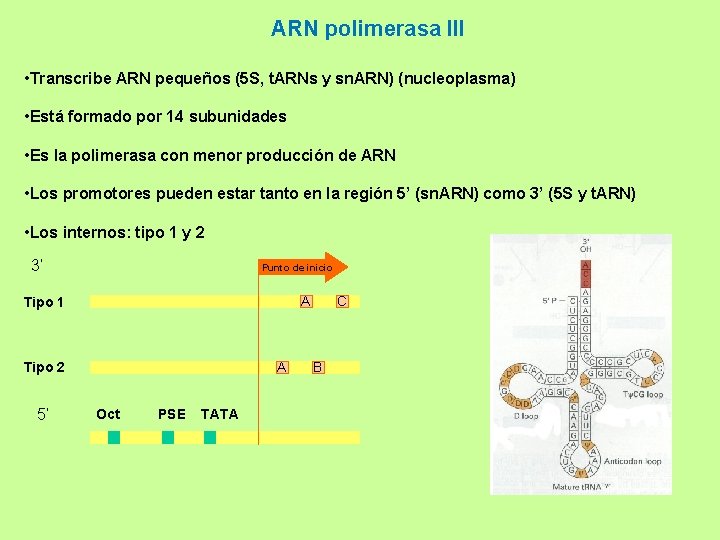
ARN polimerasa III • Transcribe ARN pequeños (5 S, t. ARNs y sn. ARN) (nucleoplasma) • Está formado por 14 subunidades • Es la polimerasa con menor producción de ARN • Los promotores pueden estar tanto en la región 5’ (sn. ARN) como 3’ (5 S y t. ARN) • Los internos: tipo 1 y 2 3’ Punto de inicio A Tipo 1 A Tipo 2 5’ Oct PSE TATA C B
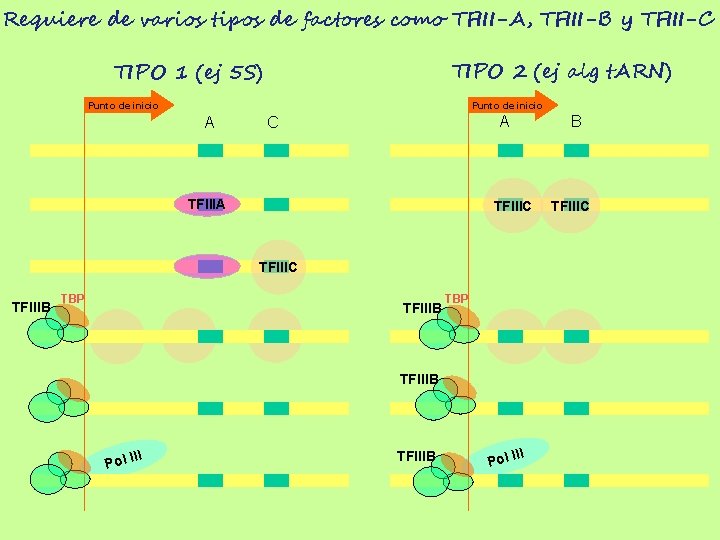
Requiere de varios tipos de factores como TFIII-A, TFIII-B y TFIII-C TIPO 2 (ej alg t. ARN) TIPO 1 (ej 5 S) Punto de inicio A A C TFIIIA TFIIIC TFIIIB TBP TFIIIB II Pol I B TFIIIC
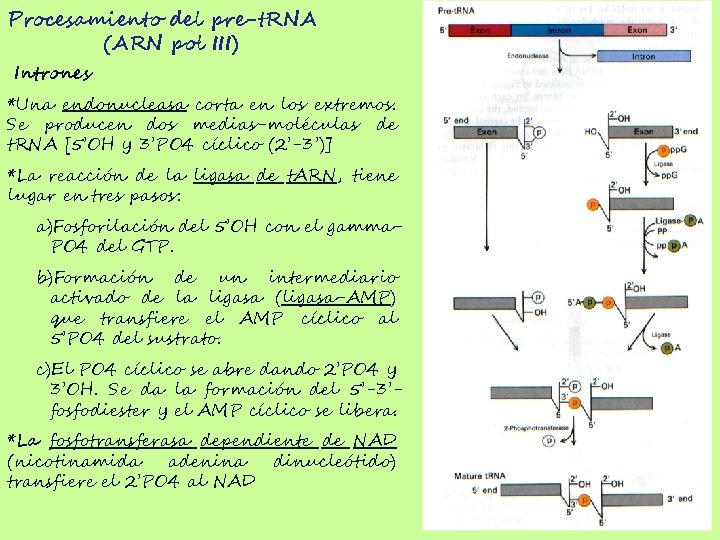
Procesamiento del pre-t. RNA (ARN pol III) Intrones *Una endonucleasa corta en los extremos. Se producen dos medias-moléculas de t. RNA [5’OH y 3’PO 4 cíclico (2’-3’)] *La reacción de la ligasa de t. ARN, tiene lugar en tres pasos: a)Fosforilación del 5’OH con el gamma. PO 4 del GTP. b)Formación de un intermediario activado de la ligasa (ligasa-AMP) que transfiere el AMP cíclico al 5’PO 4 del sustrato. c)El PO 4 cíclico se abre dando 2’PO 4 y 3’OH. Se da la formación del 5’-3’fosfodiester y el AMP cíclico se libera. *La fosfotransferasa dependiente de NAD (nicotinamida adenina dinucleótido) transfiere el 2’PO 4 al NAD
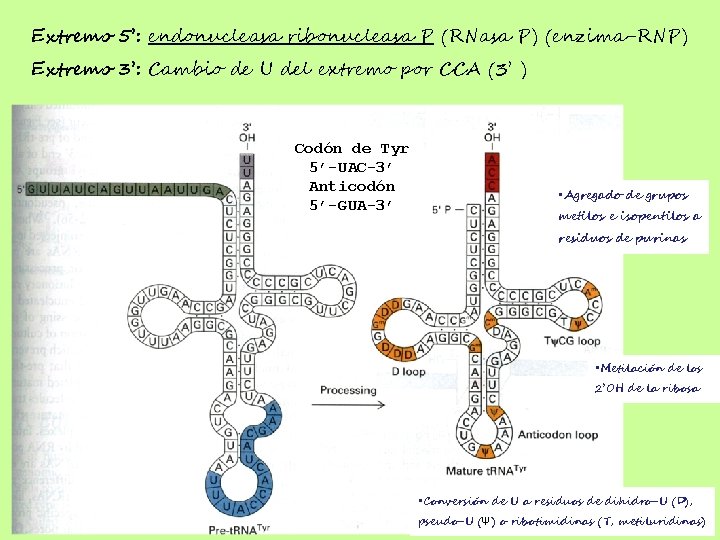
Extremo 5’: endonucleasa ribonucleasa P (RNasa P) (enzima-RNP) Extremo 3’: Cambio de U del extremo por CCA (3’ ) Codón de Tyr 5’-UAC-3’ Anticodón 5’-GUA-3’ • Agregado de grupos metilos e isopentilos a residuos de purinas • Metilación de los 2’OH de la ribosa • Conversión de U a residuos de dihidro-U (D), pseudo-U (Ψ) o ribotimidinas (T, metiluridinas)

ARN POLIMERASA II • Transcribe los genes estructurales (prot) a ARNm (y hn. ARN) (nucleoplasma). Es la enzima que transcribe la más diversa población de ARNs. • Múltiples subunidades • Se observan 3 grupos de promotores: genéricos, específicos e inducibles. • Promotores genéricos: secuencia mínima necesaria con la cual la polimerasa puede iniciar la transcripción. No depende de secuencias reguladas por tejidos. Son de baja eficiencia • Al menos 8 factores de transcripción (TFII A, B, C, D, E, F, H, J) • Condiciones generales para la síntesis de ARN Inr (región iniciadora) puede ser descrita como Py 2 CAPy 5 TATA box: secuencia consenso de 8 pb a unos ~25 pb, rodeado de secuencias ricas en GC. Lo contienen la gran mayoría de los promotores. Se une TFIID/TBP TAF: TBP-associated factors
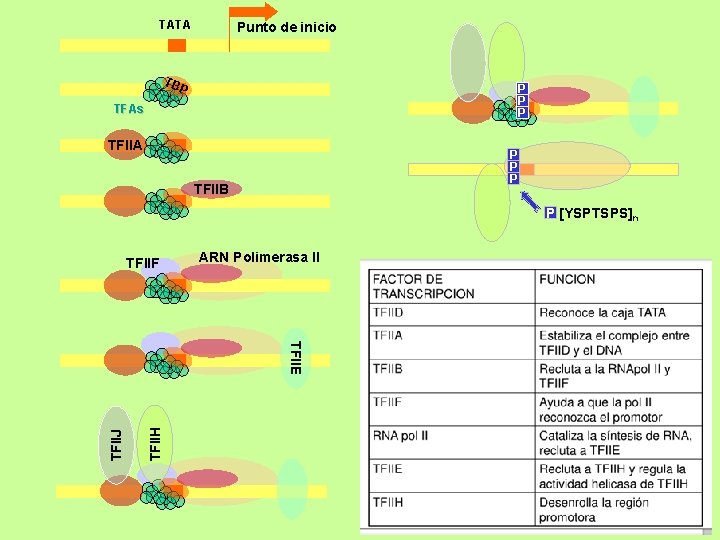
TATA Punto de inicio TB P P TFAs TFIIA P P P TFIIB P [YSPTSPS]n TFIIF ARN Polimerasa II TFIIH TFIIJ TFIIE
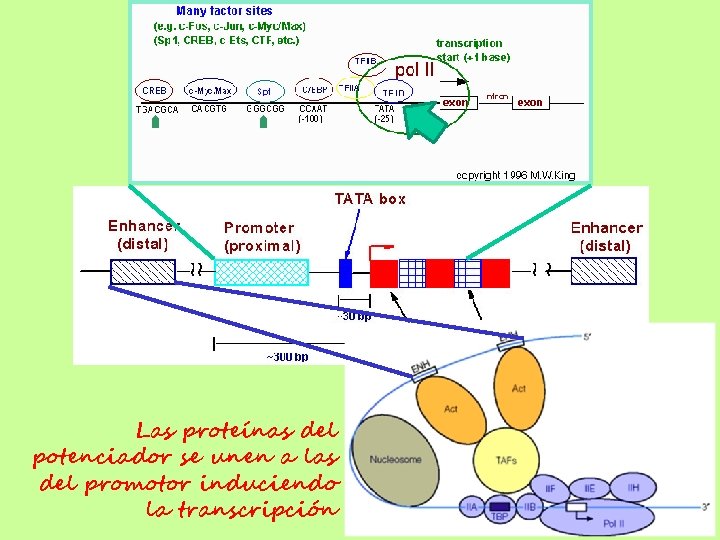
Las proteínas del potenciador se unen a las del promotor induciendo la transcripción
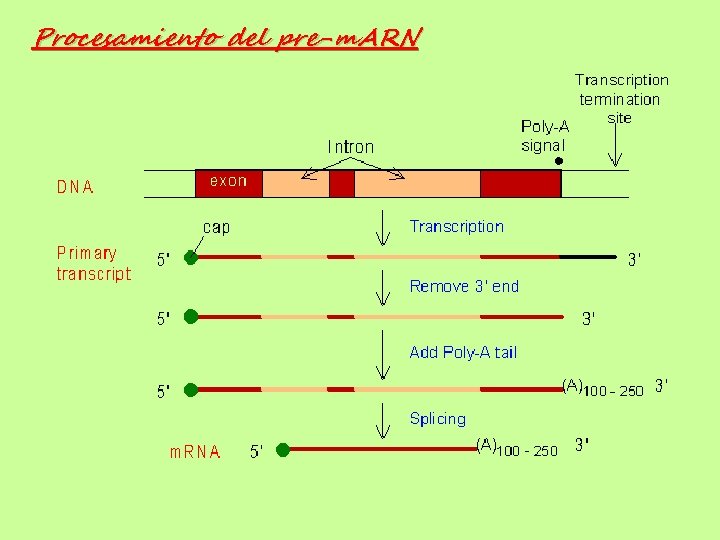
Procesamiento del pre-m. ARN
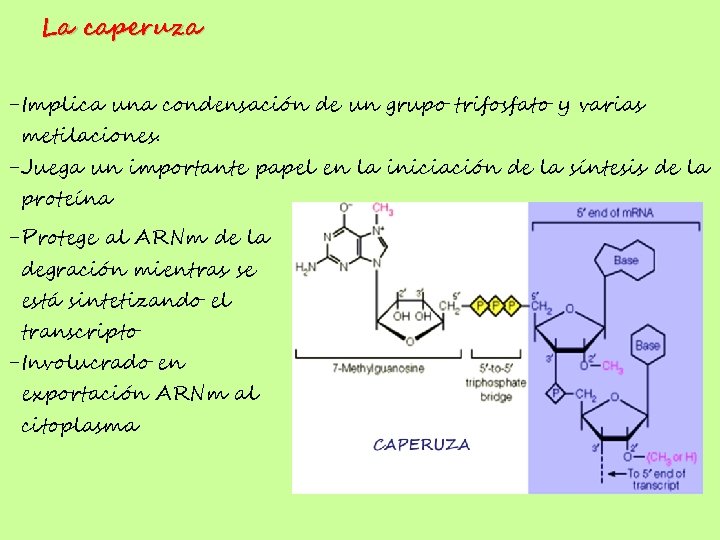
La caperuza -Implica una condensación de un grupo trifosfato y varias metilaciones. -Juega un importante papel en la iniciación de la síntesis de la proteína -Protege al ARNm de la degración mientras se está sintetizando el transcripto -Involucrado en exportación ARNm al citoplasma
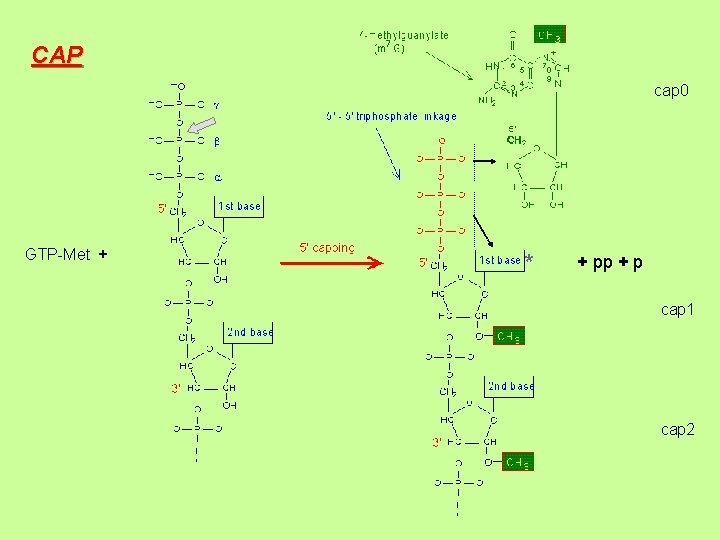
CAP cap 0 GTP-Met + * + pp + p cap 1 cap 2
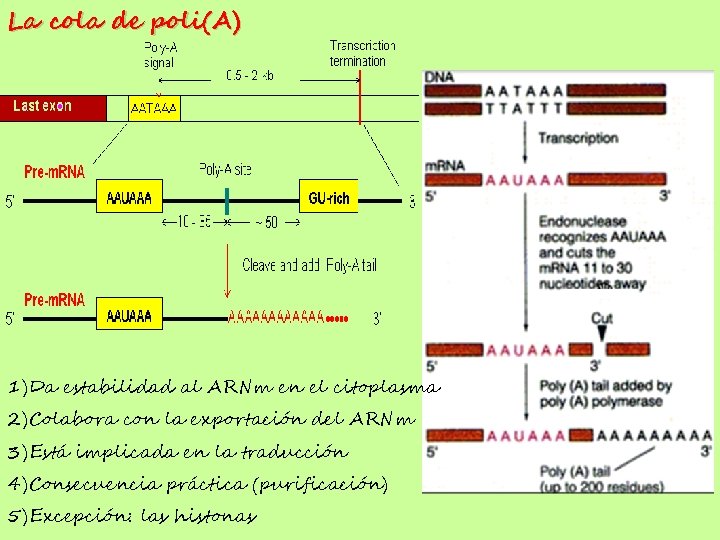
La cola de poli(A) 1) Da estabilidad al ARNm en el citoplasma 2) Colabora con la exportación del ARNm 3) Está implicada en la traducción 4) Consecuencia práctica (purificación) 5) Excepción: las histonas
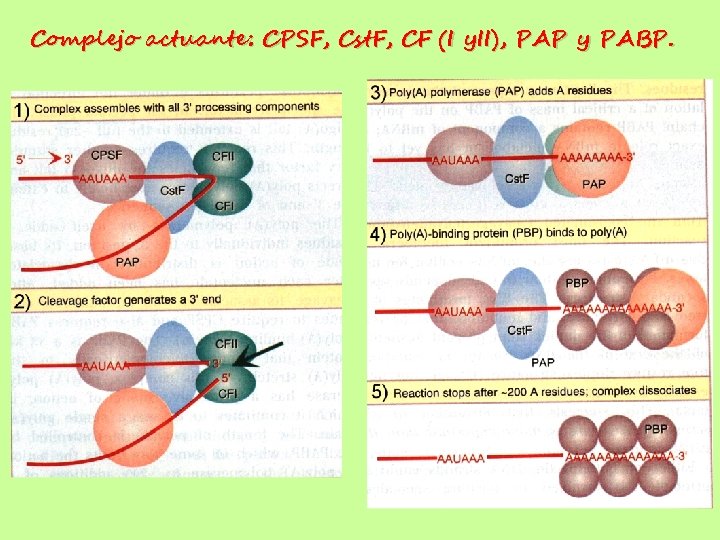
Complejo actuante: CPSF, Cst. F, CF (I y. II), PAP y PABP.
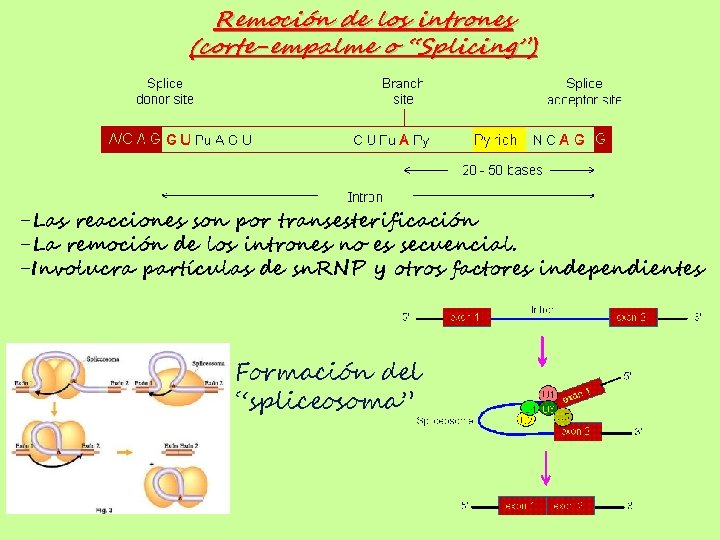
Remoción de los intrones (corte-empalme o “Splicing”) -Las reacciones son por transesterificación -La remoción de los intrones no es secuencial. -Involucra partículas de sn. RNP y otros factores independientes Formación del “spliceosoma”
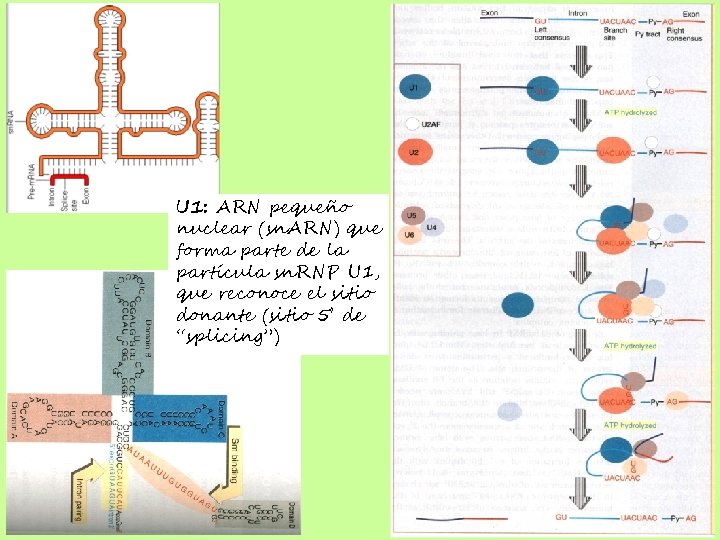
U 1: ARN pequeño nuclear (sn. ARN) que forma parte de la partícula sn. RNP U 1, que reconoce el sitio donante (sitio 5’ de “splicing”)
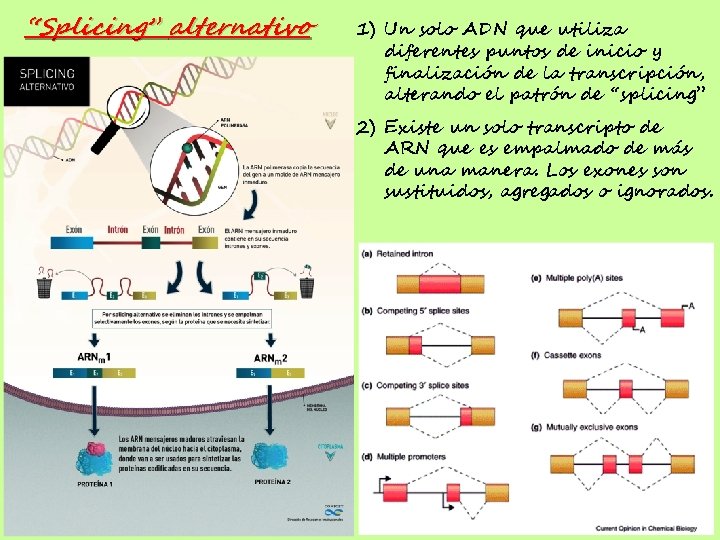
“Splicing” alternativo 1) Un solo ADN que utiliza diferentes puntos de inicio y finalización de la transcripción, alterando el patrón de “splicing” 2) Existe un solo transcripto de ARN que es empalmado de más de una manera. Los exones son sustituidos, agregados o ignorados.
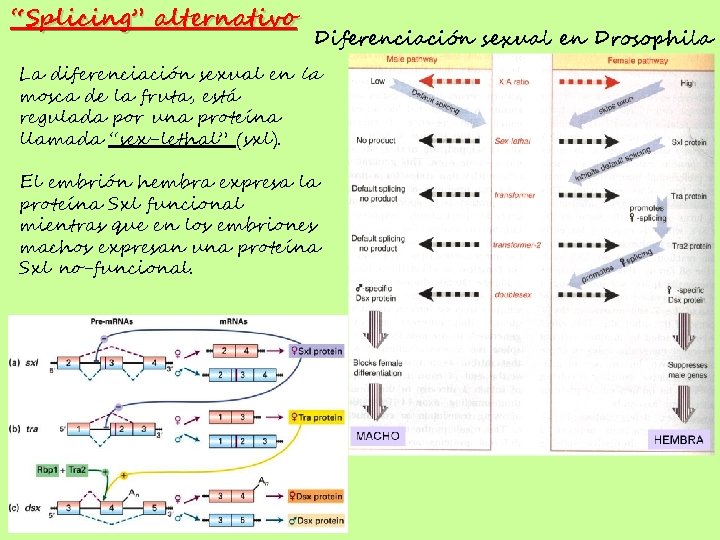
“Splicing” alternativo Diferenciación sexual en Drosophila La diferenciación sexual en la mosca de la fruta, está regulada por una proteína llamada “sex-lethal” (sxl). El embrión hembra expresa la proteína Sxl funcional mientras que en los embriones machos expresan una proteína Sxl no-funcional.
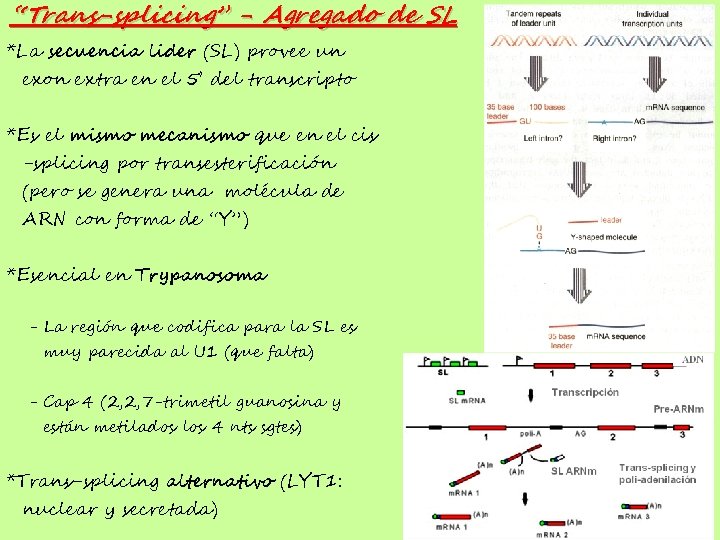
“Trans-splicing” - Agregado de SL *La secuencia lider (SL) provee un exon extra en el 5’ del transcripto *Es el mismo mecanismo que en el cis -splicing por transesterificación (pero se genera una molécula de ARN con forma de “Y”) *Esencial en Trypanosoma - La región que codifica para la SL es muy parecida al U 1 (que falta) - Cap 4 (2, 2, 7 -trimetil guanosina y están metilados los 4 nts sgtes) *Trans-splicing alternativo (LYT 1: nuclear y secretada)
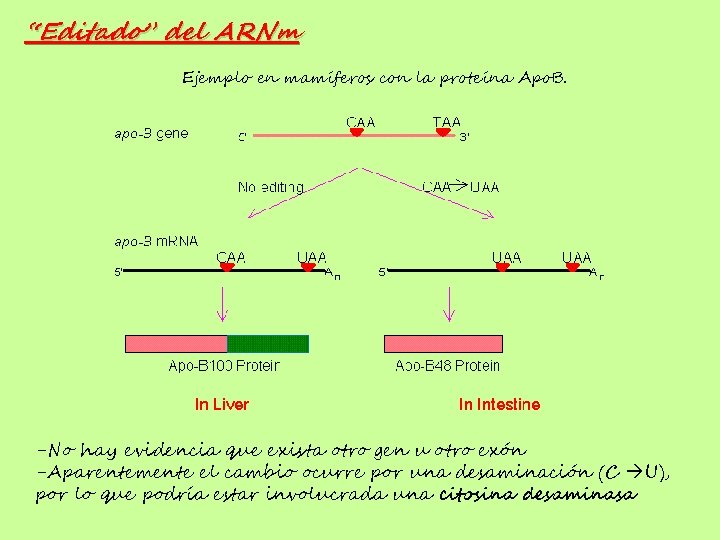
“Editado” del ARNm Ejemplo en mamíferos con la proteína Apo. B. -No hay evidencia que exista otro gen u otro exón -Aparentemente el cambio ocurre por una desaminación (C U), por lo que podría estar involucrada una citosina desaminasa
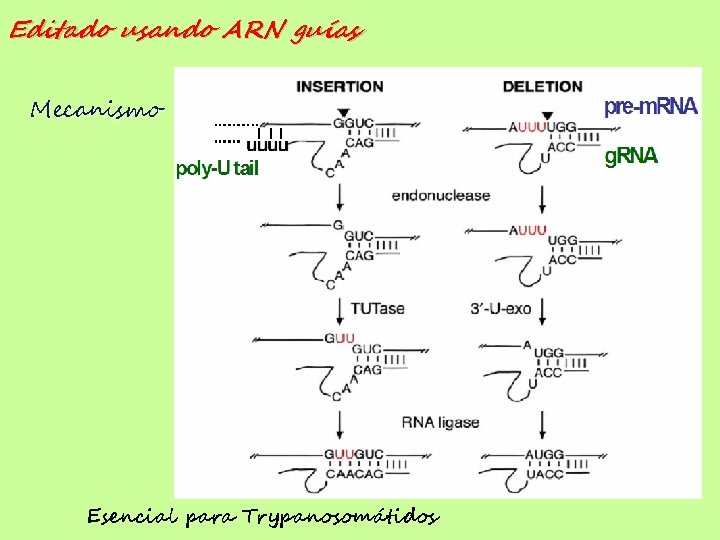
Editado usando ARN guías Mecanismo Esencial para Trypanosomátidos
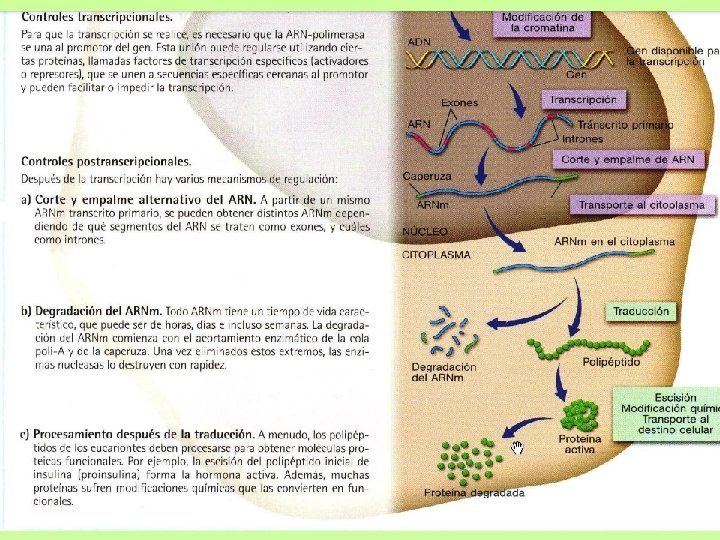

Resumen: • ARN polimerasas y esquema de sus promotores • Procesamiento de los pre-ARNr • Modificaciones en los pre-ARNt • Maduración de los pre-ARNm: • Cap • poli(A) • cis splicing (simple, alternativo) • trans splicing • Editado • Esquema de los controles en la expresión génica

¿Preguntas? ¿Dudas?
- Slides: 32