Tecnologa de ADN Recombinante Prof Javier Cabello Schomburg

Tecnología de ADN Recombinante Prof. Javier Cabello Schomburg, MS

Reflexión • Cada criatura, al nacer, nos trae el mensaje de que Dios todavía no ha perdido la esperanza en los hombres. • Rabindranath Tagore
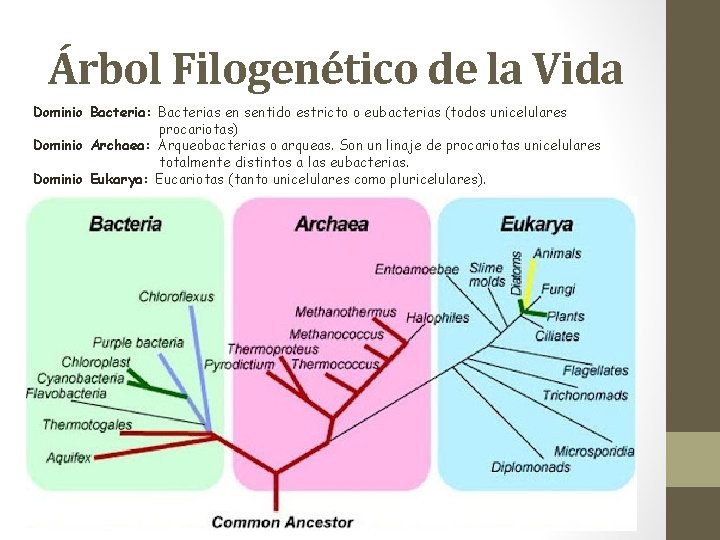
Árbol Filogenético de la Vida Dominio Bacteria: Bacterias en sentido estricto o eubacterias (todos unicelulares procariotas) Dominio Archaea: Arqueobacterias o arqueas. Son un linaje de procariotas unicelulares totalmente distintos a las eubacterias. Dominio Eukarya: Eucariotas (tanto unicelulares como pluricelulares).

¿Qué es un organismo modelo? • Son una herramienta fundamental en algunas áreas de la investigación científica, ya que permiten realizar estudios sobre determinados caracteres y los resultados pueden ser extrapolados a otras especies • Las especies que se eligen como modelo tienen las siguientes características en común: • Fácil manutención y manipulación en el laboratorio; - Ciclos de vida cortos; - Gran número de descendencia; - Disponibilidad de variabilidad fenotípica y genotípica; - Fenotipo de interés sencillo de observar o medir; - Técnicas de estudio puestas a punto para estas especies.

organismos modelo en Genética

Tecnología del ADN El genoma de un organismo es el juego completo de ADN. La planificación del Proyecto Genoma Humano se inició en 1986, previsto para el 2007. En Junio de 2000 se presentó el 90% del borrador con la secuenciación de unos 30, 000 genes y 3 millones de pares de bases (pb). Los genes son secuencias específicas de bases que codifican instrucciones para hacer proteínas. Los genes son un 2% del genoma humano. Entre una persona y otra el ADN solo difiere en 0. 2% IDENTIDAD GENÉTICA 60% De 289 genes humanos implicados en enfermedades, hay 177 cercanamente similares a los genes de Drosophila. 20% 70% 95% idéntico Humanos 30, 000 genes Chimpancé 30, 000 genes Ratón 30, 000 genes A. thaliana 25, 000 genes C. elegans 19, 000 genes R. ALEG RÍA CON D. melanogaster 13, 000 ACYT genes 2002

Enzimas de Restricción “Tijeras Moleculares”

ENDONUCLEASAS DE RESTRICCION • En 1968 se purificó la primera endonucleasa de restricción, la K 12 en E coli. • Cortaba fragmentos largos y concretos, por lo que se pensó que reconocía secuencias específicas del ADN. • Se abandonó porque aunque reconocía una zona determinada del ADN, cortaba al ADN a varias Kb de distancia. • En 1970 se aísla otra endonucleasa de restricción en Haemophilus influenzae, que reconoce y una secuencia en un duplex de ADN y la rompe en ese lugar produciendo fragmentos discretos de longitud y secuencia bien definidos.

ENDONUCLEASAS DE RESTRICCION Fenómeno de restricción: reconocimiento por parte de una bacteria de un ADN extraño y lisis del mismo en pequeños fragmentos. El fenómeno de restricción se descubrió en E coli, cuando se hizo crecer el bacteriófago lambda. Si la bacteria crece encontraremos varias colonias por placa. Si no crece, no encontaremos colonias. En la cepa C de E coli crecía bien el bacteriófago , pero si este se crecía en la cepa K o la R, la eficiencia de crecimiento era mucho menor o nula. El fago era restringido por esta cepa.
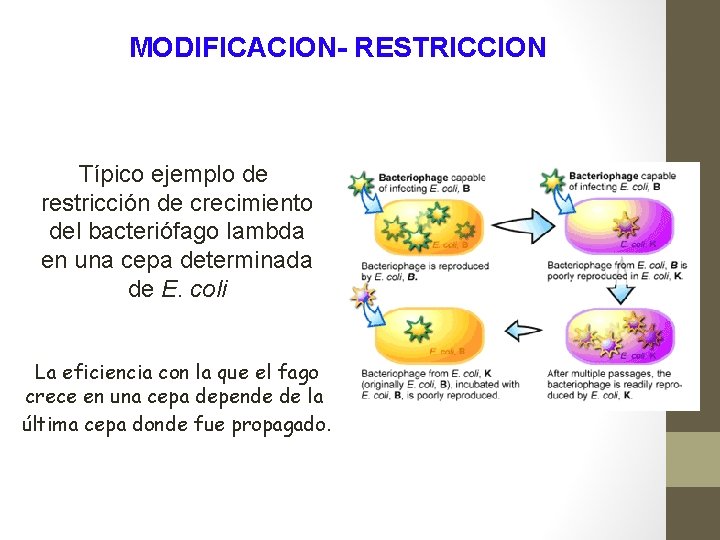
MODIFICACION- RESTRICCION Típico ejemplo de restricción de crecimiento del bacteriófago lambda en una cepa determinada de E. coli La eficiencia con la que el fago crece en una cepa depende de la última cepa donde fue propagado.

MODIFICACION- RESTRICCION Explicación: El DNA del fago es degradado en cuanto se incorpora, y a la endonucleasa responsable de esta degradación se le llama endonucleasa de restricción o enzima de restricción. El huésped restrictivo debe proteger a su propio ADN de la acción de las enzimas de restricción y para ello modifica a su propio ADN. Modificación: metilación de ciertas bases en un número muy limitado, justo en los lugares de reconocimiento de las enzimas de restricción. El DNA del fago que sobrevive algún ciclo en el huésped restrictivo se replica y también es metilado por las metilasas de la bacteria, y por tanto modificado y protegido, y puede crecer bien en una nueva reinfección.
METILACION Y RESTRICCION
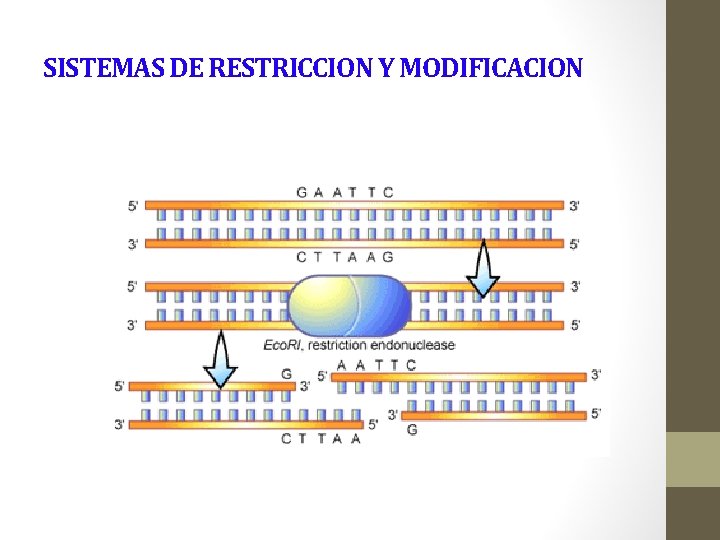
SISTEMAS DE RESTRICCION Y MODIFICACION

SISTEMAS DE RESTRICCION Y MODIFICACION Nomenclatura: Tres letras: 1 a letra de género de la bacteria donde se encontró 2 a y 3 a letras especie de la bacteria donde se encontró Letra de la cepa donde se produce la enzima de restricción (si es alguna cepa especial) Si en la misma bacteria hay varios sistemas de restricción, se especifica por números romanos.
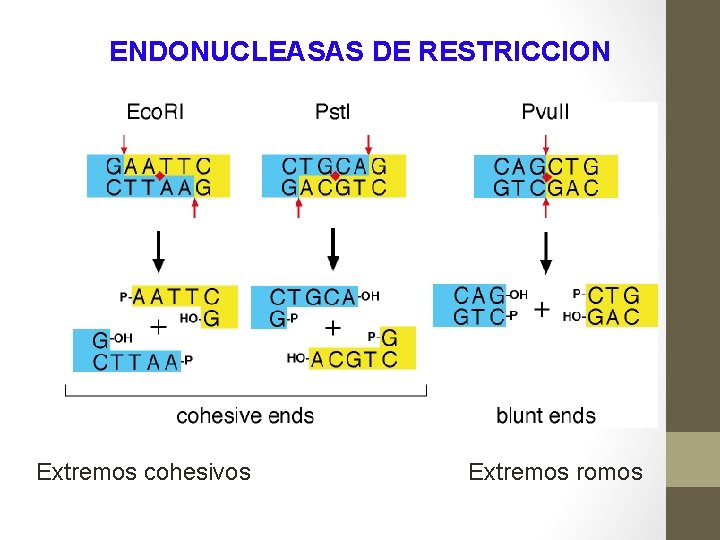
ENDONUCLEASAS DE RESTRICCION Extremos cohesivos Extremos romos
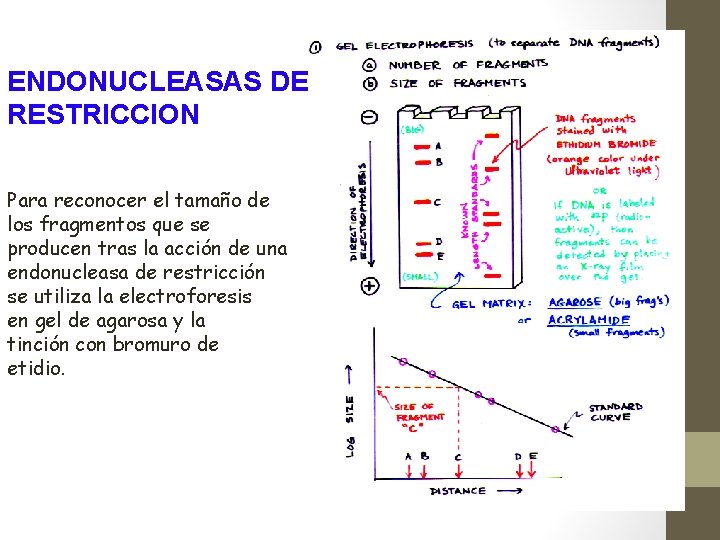
ENDONUCLEASAS DE RESTRICCION Para reconocer el tamaño de los fragmentos que se producen tras la acción de una endonucleasa de restricción se utiliza la electroforesis en gel de agarosa y la tinción con bromuro de etidio.

ENDONUCLEASAS DE RESTRICCION Se han estudiado 10, 000 bacterias para Encontrar enzimas de restricción. Se han encontrado 3, 000 enzimas de Restricción específicas para aproximada mente 200 secuencias de ADN. Las enzimas diferentes que tienen especificidad por la misma secuencia de ADN y que cortan en el mismo sitio se les llama isoschizomeros. Si reconocen la misma secuencia pero cortan en diferente lugar al ADN se les denomina neoeschizomeros. www. rebase. neb. com

ENDONUCLEASAS DE RESTRICCION El número y el tamaño de fragmentos de ADN generados por una enzima de restricción depende de la frecuencia de aparición De los lugares diana en el ADN. Teóricamente, si tenemos un ADN que sea: - 50% de frecuencia de C+G - las cuatro bases distribuidas al azar El número de cortes en sería cada: si la secuencia diana es de 4 bases corte cada 4 4(256) bases si la secuencia diana es de 6 bases corte cada 4 6 (4096) bases En la práctica, no ocurre exactamente así.

ENDONUCLEASAS DE RESTRICCIÓN § Son nucleasas que reconocen las moléculas de ADN en sitios determinados, por medio del reconocimiento de secuencias específicas § Las secuencias de reconocimiento son palindrómicas § Tipos de endonucleasas de restricción: • tipo. I y III: cortan el ADN en sitios poco específicos y distantes del sitio de reconocimiento • tipo II: cortan las dos hebras de DNA en puntos equivalentes, muy específicos, dentro de la secuencia de reconocimiento. Son las más útiles en ingeniería genética. § Eco. RI: efectúa cortes escalonados en la secuencia palindrómica específica de 6 pb Eco. RI § Eco. RI: genera fragmentos complementarios de hebra simple denominados fragmentos de restricción con extremos cohesivos
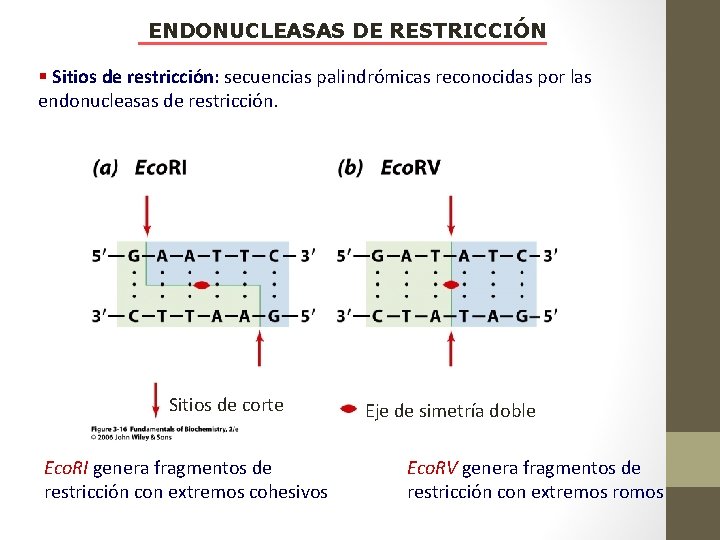
ENDONUCLEASAS DE RESTRICCIÓN § Sitios de restricción: secuencias palindrómicas reconocidas por las endonucleasas de restricción. Sitios de corte Eco. RI genera fragmentos de restricción con extremos cohesivos Eje de simetría doble Eco. RV genera fragmentos de restricción con extremos romos

ENDONUCLEASAS DE RESTRICCIÓN § Nomenclatura: mediante tres letras tomadas del género y la especie de la bacteria de la que se aislaron originalmente, seguida de una letra que indica el serotipo y un nº romano, en el caso de haber encontrado diferentes enzimas en una misma variente § Se han caracterizado más de 3000 enzimas de restricción de tipo II con más de 200 secuencias de reconocimiento diferentes.
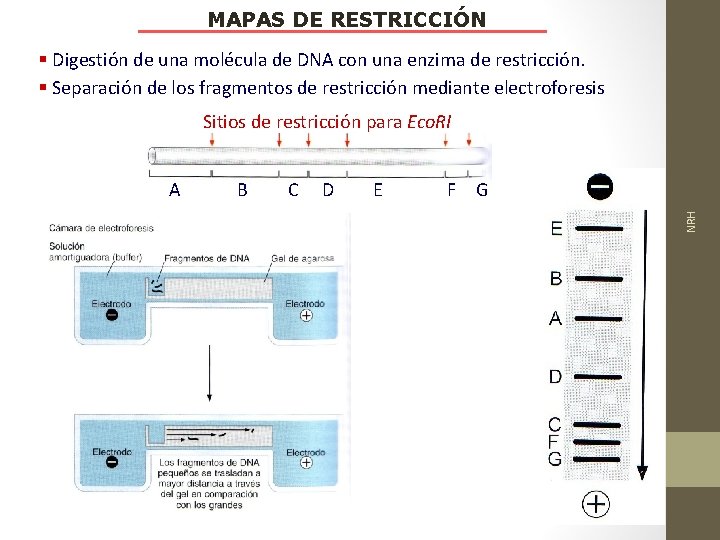
MAPAS DE RESTRICCIÓN § Digestión de una molécula de DNA con una enzima de restricción. § Separación de los fragmentos de restricción mediante electroforesis Sitios de restricción para Eco. RI B C D E F G NRH A
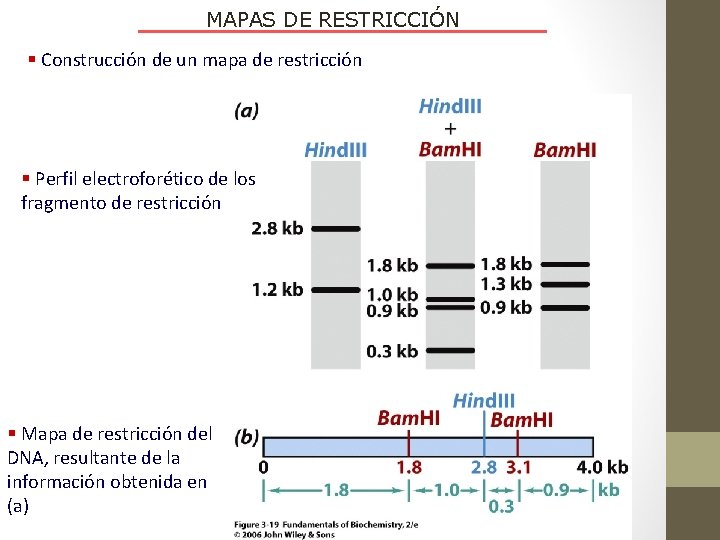
MAPAS DE RESTRICCIÓN § Construcción de un mapa de restricción § Perfil electroforético de los fragmento de restricción § Mapa de restricción del DNA, resultante de la información obtenida en (a)
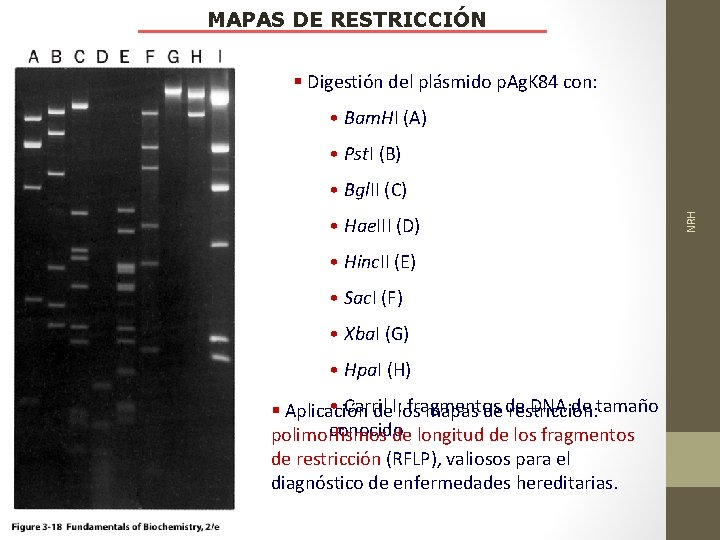
MAPAS DE RESTRICCIÓN § Digestión del plásmido p. Ag. K 84 con: • Bam. HI (A) • Pst. I (B) • Hae. III (D) • Hinc. II (E) • Sac. I (F) • Xba. I (G) • Hpa. I (H) • Carril fragmentos DNA de tamaño § Aplicación de. I: los mapas de de restricción: conocido polimorfismos de longitud de los fragmentos de restricción (RFLP), valiosos para el diagnóstico de enfermedades hereditarias. NRH • Bgl. II (C)
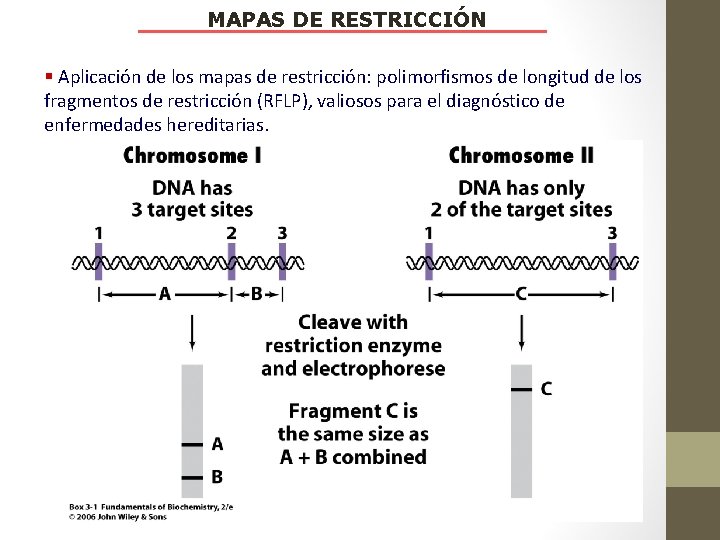
MAPAS DE RESTRICCIÓN § Aplicación de los mapas de restricción: polimorfismos de longitud de los fragmentos de restricción (RFLP), valiosos para el diagnóstico de enfermedades hereditarias.

Vectores de clonación § Los vectores de clonación son moléculas pequeñas de DNA que se replican de manera autónoma § Tipos de vectores • Plásmidos Ø moléculas de DNA circular que se encuentran en bacterias o levaduras Ø se pueden clonar fragmentos de DNA de no más de 10 kpb • Bacteriófagos Ø fagos que infectan bacterias Ø se pueden clonar fragmentos de DNA de hasta 16 kpb • Cromosomas artificiales bacterianos (BAC) y de levaduras (YAC) Ø se pueden clonar fragmentos de DNA de hasta varios cientos de kpb
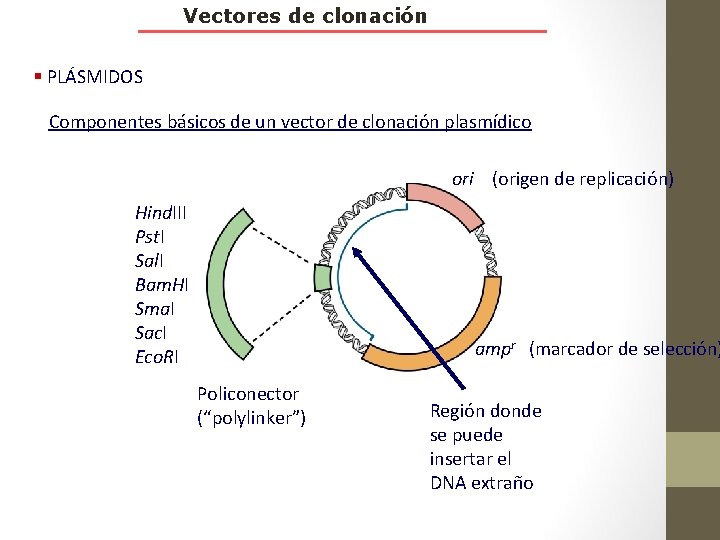
Vectores de clonación § PLÁSMIDOS Componentes básicos de un vector de clonación plasmídico ori (origen de replicación) Hind. III Pst. I Sal. I Bam. HI Sma. I Sac. I Eco. RI ampr (marcador de selección) Policonector (“polylinker”) Región donde se puede insertar el DNA extraño
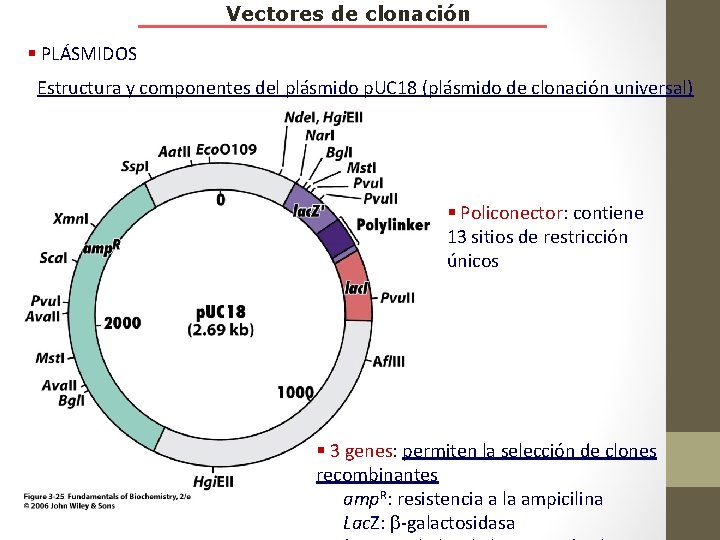
Vectores de clonación § PLÁSMIDOS Estructura y componentes del plásmido p. UC 18 (plásmido de clonación universal) § Policonector: contiene 13 sitios de restricción únicos § 3 genes: permiten la selección de clones recombinantes amp. R: resistencia a la ampicilina Lac. Z: b-galactosidasa
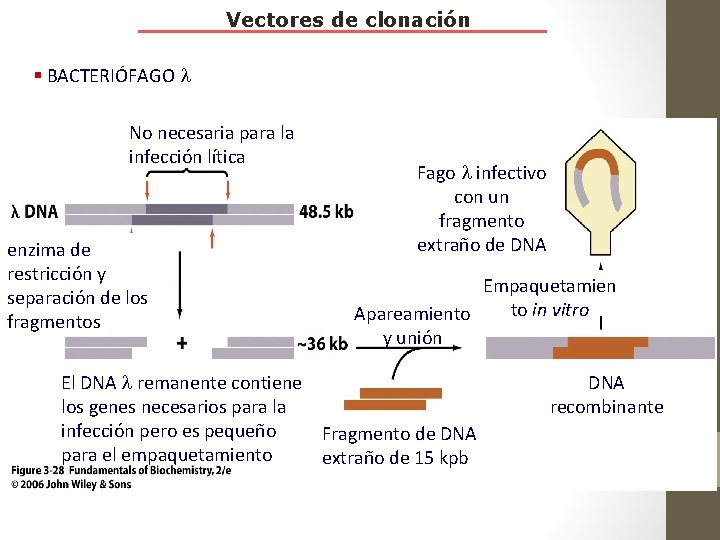
Vectores de clonación § BACTERIÓFAGO No necesaria para la infección lítica enzima de restricción y separación de los fragmentos Fago infectivo con un fragmento extraño de DNA Empaquetamien to in vitro Apareamiento y unión El DNA remanente contiene los genes necesarios para la infección pero es pequeño Fragmento de DNA para el empaquetamiento extraño de 15 kpb DNA recombinante
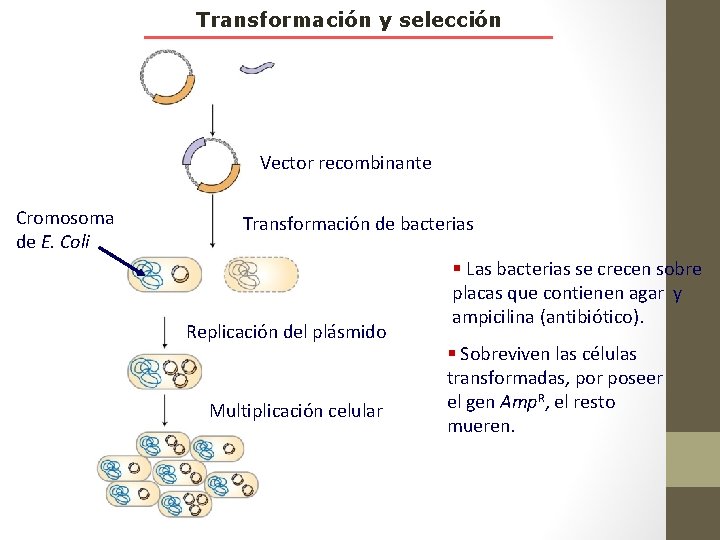
Transformación y selección Vector recombinante Cromosoma de E. Coli Transformación de bacterias Replicación del plásmido Multiplicación celular § Las bacterias se crecen sobre placas que contienen agar y ampicilina (antibiótico). § Sobreviven las células transformadas, por poseer el gen Amp. R, el resto mueren.
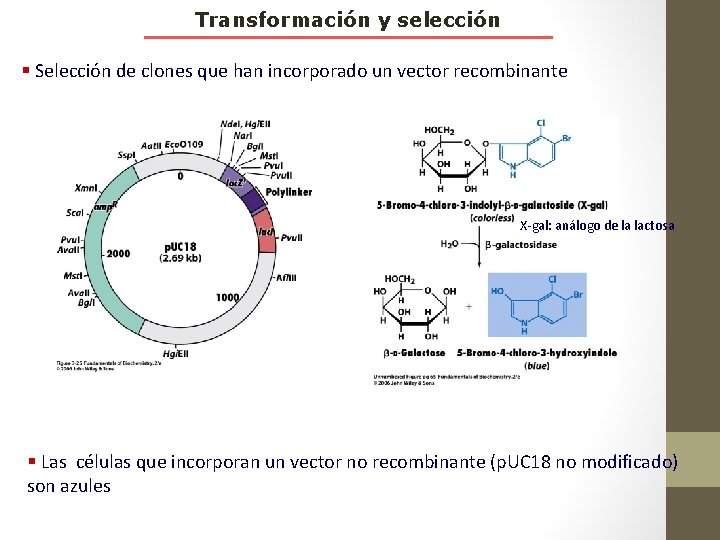
Transformación y selección § Selección de clones que han incorporado un vector recombinante X-gal: análogo de la lactosa § Las células que incorporan un vector no recombinante (p. UC 18 no modificado) son azules

Biblioteca de ADN Biblioteca genómica colección de clones formados a partir de todos los fragmentos de ADN del genoma de una especie, tejido o tipo celular. Biblioteca de ADN genómico los fragmentos de ADN provienen de la escisión del genoma. Contiene regiones codificantes y no codificantes. Se genera por clonación de fragmentos genómicos al azar. Biblioteca de c. ADN los fragmentos provienen de los m. ARNs retrotranscritos. Contiene sólo las secuencias expresadas de un tipo particular de célula.
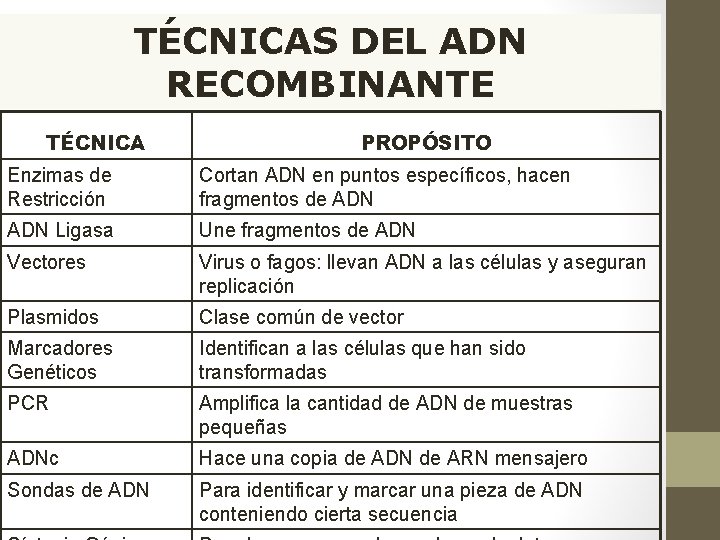
TÉCNICAS DEL ADN RECOMBINANTE TÉCNICA PROPÓSITO Enzimas de Restricción Cortan ADN en puntos específicos, hacen fragmentos de ADN Ligasa Une fragmentos de ADN Vectores Virus o fagos: llevan ADN a las células y aseguran replicación Plasmidos Clase común de vector Marcadores Genéticos Identifican a las células que han sido transformadas PCR Amplifica la cantidad de ADN de muestras pequeñas ADNc Hace una copia de ADN de ARN mensajero Sondas de ADN Para identificar y marcar una pieza de ADN conteniendo cierta secuencia
m. ARNs ADN Construcción de Bibliotecas de c. ADN
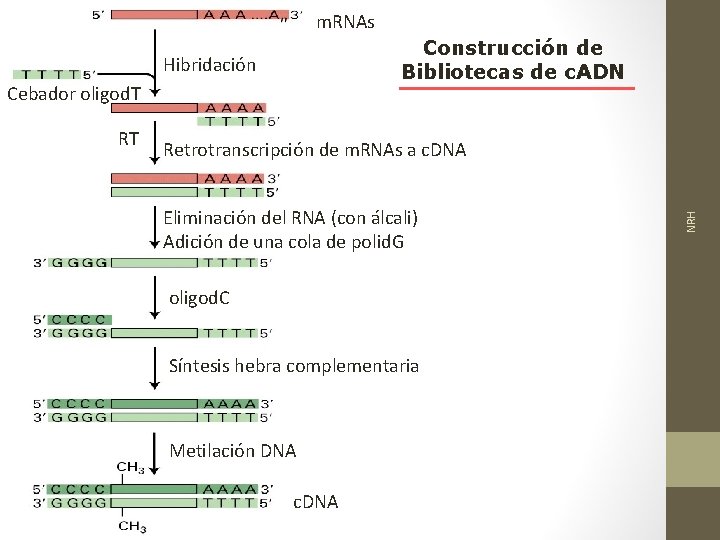
m. RNAs Construcción de Bibliotecas de c. ADN Hibridación Cebador oligod. T Retrotranscripción de m. RNAs a c. DNA Eliminación del RNA (con álcali) Adición de una cola de polid. G oligod. C Síntesis hebra complementaria Metilación DNA c. DNA NRH RT
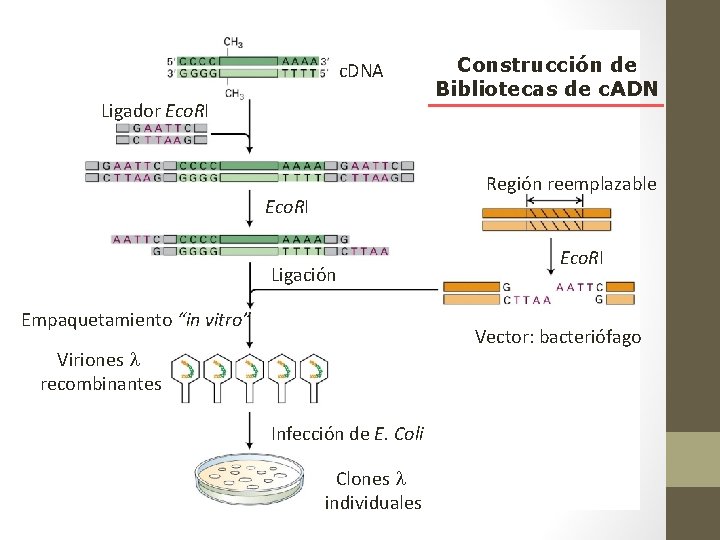
c. DNA Ligador Eco. RI Construcción de Bibliotecas de c. ADN Región reemplazable Eco. RI Ligación Empaquetamiento “in vitro” Eco. RI Vector: bacteriófago Viriones recombinantes Infección de E. Coli Clones individuales

Cribado de la genoteca 1) Las colonias se transfieren desde una placa de cultivo a un filtro de nitrocelulosa 2) Tratamiento del filtro con álcali y posterior secado; el DNA desnaturalizado queda unido al filtro 3) Apareamiento con una sonda marcada radiactivamente; formación de híbridos con su DNA complementario 4) Autorradiografía 1 2 3 4 NRH § Hibridación de colonias “in situ” Colonias detectadas por la sonda
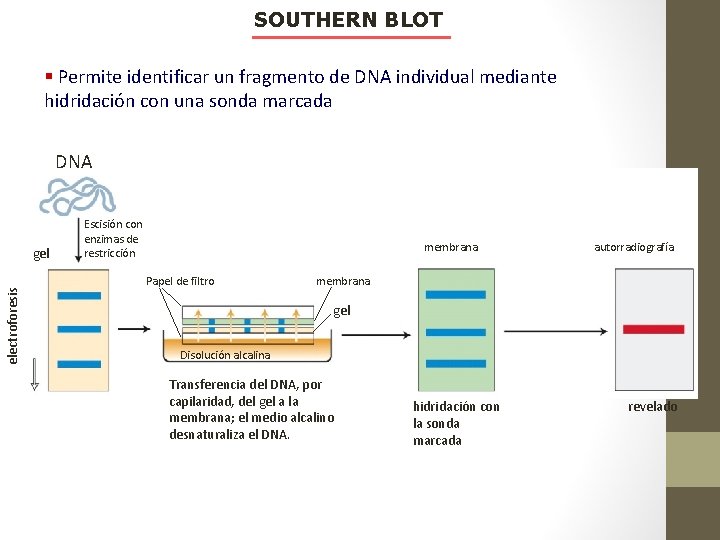
SOUTHERN BLOT § Permite identificar un fragmento de DNA individual mediante hidridación con una sonda marcada DNA electroforesis gel Escisión con enzimas de restricción membrana Papel de filtro autorradiografía membrana gel Disolución alcalina Transferencia del DNA, por capilaridad, del gel a la membrana; el medio alcalino desnaturaliza el DNA. hidridación con la sonda marcada revelado
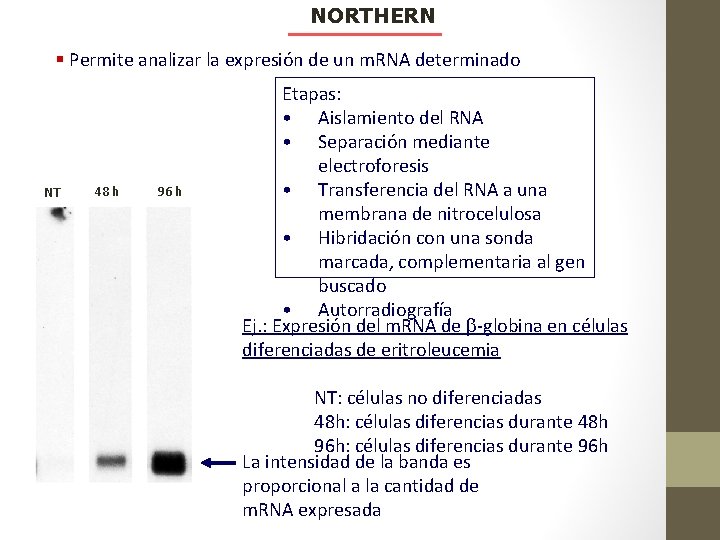
NORTHERN § Permite analizar la expresión de un m. RNA determinado NT 48 h 96 h Etapas: • Aislamiento del RNA • Separación mediante electroforesis • Transferencia del RNA a una membrana de nitrocelulosa • Hibridación con una sonda marcada, complementaria al gen buscado • Autorradiografía Ej. : Expresión del m. RNA de b-globina en células diferenciadas de eritroleucemia NT: células no diferenciadas 48 h: células diferencias durante 48 h 96 h: células diferencias durante 96 h La intensidad de la banda es proporcional a la cantidad de m. RNA expresada

PCR § PCR: reacción en cadena de la polimerasa (polymerase chain reaction) § Permite amplificar regiones de DNA de secuencias conocidas cebador Etapas: • Desnaturalización del DNA: 95ºC • Hibridación con un exceso de cebadores: 50 - 60ºC Cebador: oligonucleótido de 18 -20 nt de longitud Tienen secuencia complementaria a los extremos 3’ del segmento de DNA de interés 3) Síntesis de DNA: 72 ºC Taq polimerasa (Thermus aquaticus, bacteria de aguas termales) Estas etapas se repiten entre 20 a 30 veces

PCR Ciclo 1 Desnaturalización Hidridación Ciclo 3 Desnaturalización Hidridación Síntesis Ciclo 2 Desnaturalización Hidridación Síntesis Ciclos 4, 5, 6, etc… La secuencia deseada (delimitada por los cebadores) se incrementa exponencialmente, alrededor de un millón de veces después de 20 ciclos; el resto de secuencias en la muestra de DNA original permanece sin amplificar.
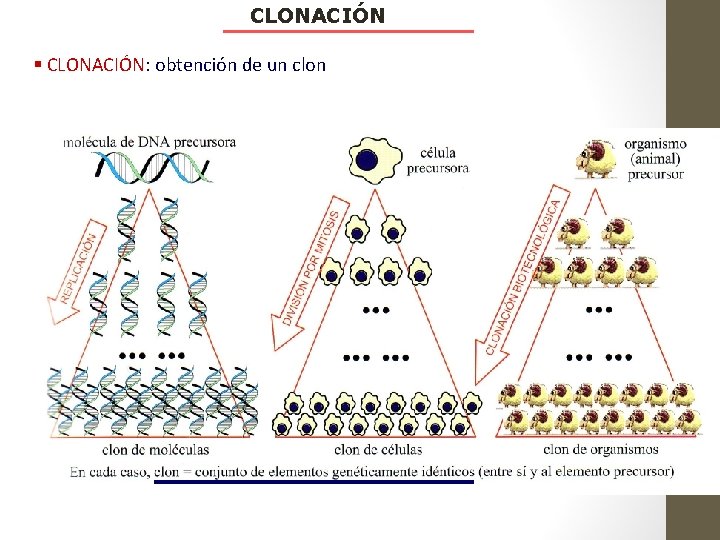
CLONACIÓN § CLONACIÓN: obtención de un clon
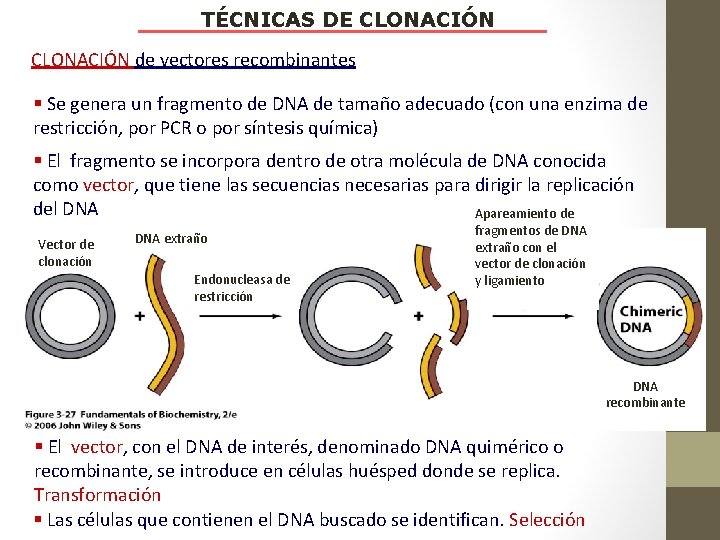
TÉCNICAS DE CLONACIÓN de vectores recombinantes § Se genera un fragmento de DNA de tamaño adecuado (con una enzima de restricción, por PCR o por síntesis química) § El fragmento se incorpora dentro de otra molécula de DNA conocida como vector, que tiene las secuencias necesarias para dirigir la replicación del DNA Apareamiento de Vector de clonación DNA extraño Endonucleasa de restricción fragmentos de DNA extraño con el vector de clonación y ligamiento DNA recombinante § El vector, con el DNA de interés, denominado DNA quimérico o recombinante, se introduce en células huésped donde se replica. Transformación § Las células que contienen el DNA buscado se identifican. Selección
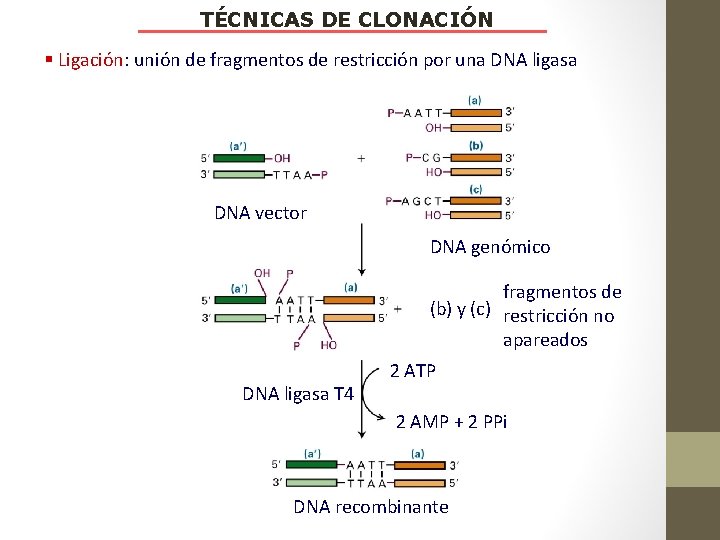
TÉCNICAS DE CLONACIÓN § Ligación: unión de fragmentos de restricción por una DNA ligasa DNA vector DNA genómico fragmentos de (b) y (c) restricción no apareados DNA ligasa T 4 2 ATP 2 AMP + 2 PPi DNA recombinante
- Slides: 44