Struktury molekularne Bioinformatyczne metody wizualizacji formaty plikw przewidywanie

Struktury molekularne Bioinformatyczne metody wizualizacji, formaty plików, przewidywanie struktur biomolekuł (na przykładzie białek). Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 1
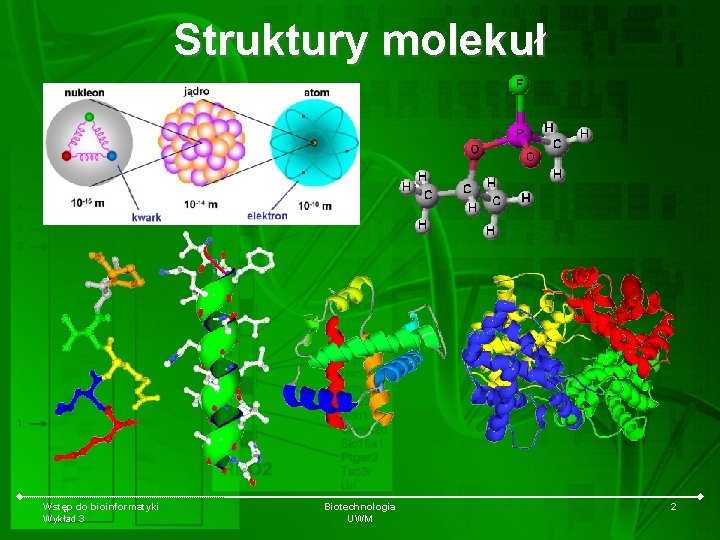
Struktury molekuł Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 2

Przykładowe formaty plików Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 3

Model struktury pierwszorzędowej białka Plik w formacie FASTA >gi|5524211|gb|AAD 44166. 1| cytochrome b [Elephas maximus] LCLYTHIGRNIYYGSYLYSETWNTGIMLLLITMATAFMGYVLPWGQMSFWGATVITNLFSAIPYIGTNLV EWIWGGFSVDKATLNRFFAFHFILPFTMVALAGVHLTFLHETGSNNPLGLTSDSDKIPFHPYYTIKDFLG LLILILLLLLLALLSPDMLGDPDNHMPADPLNTPLHIKPEWYFLFAYAILRSVPNKLGGVLALFLSIVIL GLMPFLHTSKHRSMMLRPLSQALFWTLTMDLLTLTWIGSQPVEYPYTIIGQMASILYFSIILAFLPIAGX IENY >nazwa_sekwencji_1 sek. WENCJAdan. EGObia. LKAlubni. CInuk. LEOTYDOWEJ >nazwa_sekwencji_2 kol. EJNAsek. WENCJAdow. OLNEGOwyb. RANEGOBIALKAlubnici. DNA >kolejna itd Kryteria formatu FASTA: - Tylko sekwencja lub sekwencja z opisem - Opis danej sekwencji w oddzielnej linijce (powyżej) i poprzedzony znakiem „>” - Sekwencja TYLKO z dozwolonych znaków dowolnej wielkości - Każda linijka sekwencji maksymalnie do 80 znaków Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 4

Dozwolone symbole w formacie FASTA A C G T U R Y K --> --> adenosine cytidine guanine thymidine uridine G A (purine) T C (pyrimidine) G T (keto) M S W B D H V N - --> A C --> G C --> A T --> G A --> A C --> G C --> A G gap of (amino) (strong) (weak) C T T A C T (any) indeterminate length For those programs that use amino acid query sequences (BLASTP and TBLASTN), the accepted amino acid codes are: A B C D E F G H I K L M alanine aspartate or asparagine cystine aspartate glutamate phenylalanine glycine histidine isoleucine lysine leucine methionine Wstęp do bioinformatyki Wykład 3 P Q R S T U V W Y Z X * proline glutamine arginine serine threonine selenocysteine valine tryptophan tyrosine glutamate or glutamine any translation stop Biotechnologia UWM 5
![Format FASTA >gi|49472664|gb|AAT 66182. 1| cytochrome c oxidase subunit III [Homo sapiens] MTHQSHAYHMVKPSPWPLTGALSALLMTSGLAMWFHFHSMTLLMLGLLTNTLTMYQWWRDVTRESTYQGH HTPPVQKGLRYGMILFITSEVFFFAGFFWAFYHSSLAPTPQLGGHWPPTGITPLNPLEVPLLNTSVLLAS Format FASTA >gi|49472664|gb|AAT 66182. 1| cytochrome c oxidase subunit III [Homo sapiens] MTHQSHAYHMVKPSPWPLTGALSALLMTSGLAMWFHFHSMTLLMLGLLTNTLTMYQWWRDVTRESTYQGH HTPPVQKGLRYGMILFITSEVFFFAGFFWAFYHSSLAPTPQLGGHWPPTGITPLNPLEVPLLNTSVLLAS](http://slidetodoc.com/presentation_image/214bf36037484ddce3221f003d6cab89/image-6.jpg)
Format FASTA >gi|49472664|gb|AAT 66182. 1| cytochrome c oxidase subunit III [Homo sapiens] MTHQSHAYHMVKPSPWPLTGALSALLMTSGLAMWFHFHSMTLLMLGLLTNTLTMYQWWRDVTRESTYQGH HTPPVQKGLRYGMILFITSEVFFFAGFFWAFYHSSLAPTPQLGGHWPPTGITPLNPLEVPLLNTSVLLAS GVSITWAHHSLMENNRNQMIQALLITILLGLYFTLLQASEYFESPFTISDGIYGSTFFVATGFHGLHVII GSTFLTICFIRQLMFHFTSKHHFGFEAAAWYWHFVDVVWLFLYVSIYWWGS --------------------------------------------------------------1 61 121 181 mthqshayhm vtrestyqgh itplnplevp yfespftisd vkpspwpltg htppvqkglr llntsvllas giygstffva alsallmtsg ygmilfitse gvsitwahhs tgfhglhvii lamwfhfhsm vfffagffwa lmennrnqmi gstflticfi tllmlglltn fyhsslaptp qallitillg rqlmfhftsk tltmyqwwrd qlgghwpptg lyftllqase hhfgfeaaaw 241 ywhfvdvvwl flyvsiywwg s Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 6
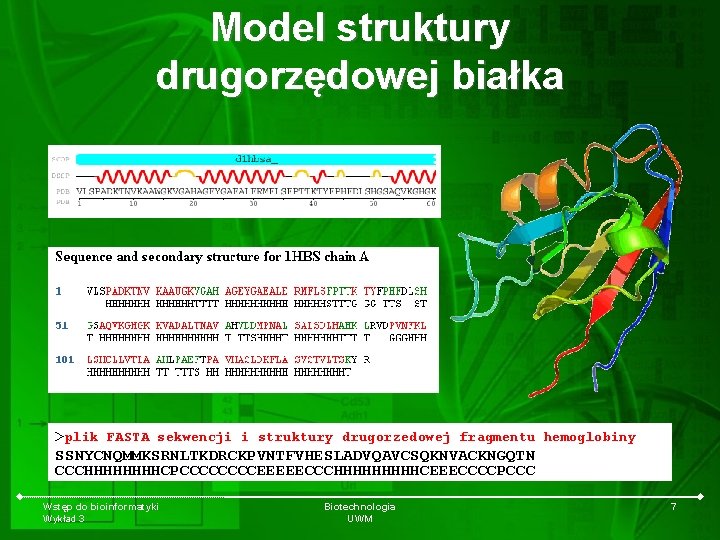
Model struktury drugorzędowej białka >plik FASTA sekwencji i struktury drugorzedowej fragmentu hemoglobiny SSNYCNQMMKSRNLTKDRCKPVNTFVHESLADVQAVCSQKNVACKNGQTN CCCHHHHCPCCCCEEEEECCCHHHHHCEEECCCCPCCC Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 7

Struktury drugorzędowe • Helisy – – – prawoskrętna lewoskrętna 3 -turn helix (3/10 helix). Min length 3 residues (G) 4 -turn helix (alpha helix). Min length 4 residues (H) 5 -turn helix (pi helix). Min length 5 residues (I) • Beta-kartki (E) – równoległe – anty-równoległe – PSI-loop • • Zwroty (spinki) stabilizowane wiązaniami wodorowymi (3, 4 lub 5 turn) (T) Nitka – struktura dowolna, nieokreślona (C) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 8
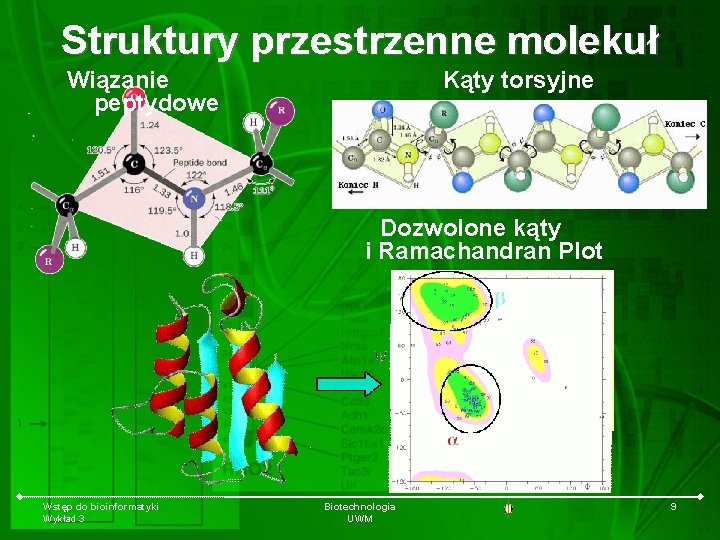
Struktury przestrzenne molekuł Wiązanie peptydowe Kąty torsyjne Dozwolone kąty i Ramachandran Plot Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 9
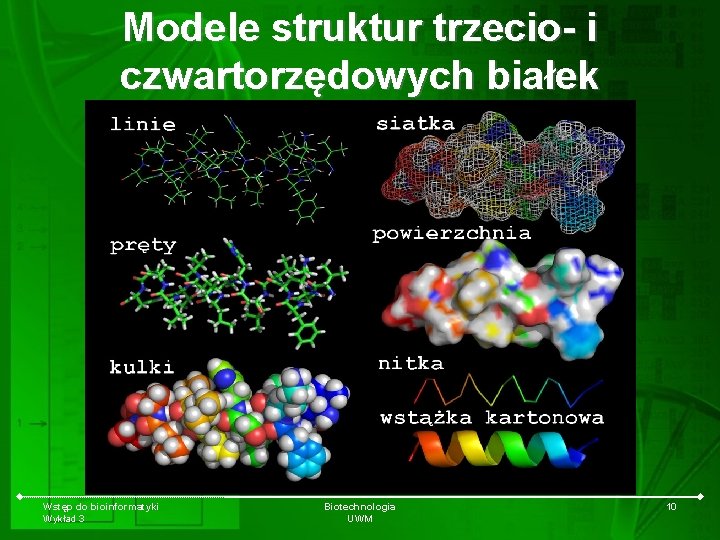
Modele struktur trzecio- i czwartorzędowych białek Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 10
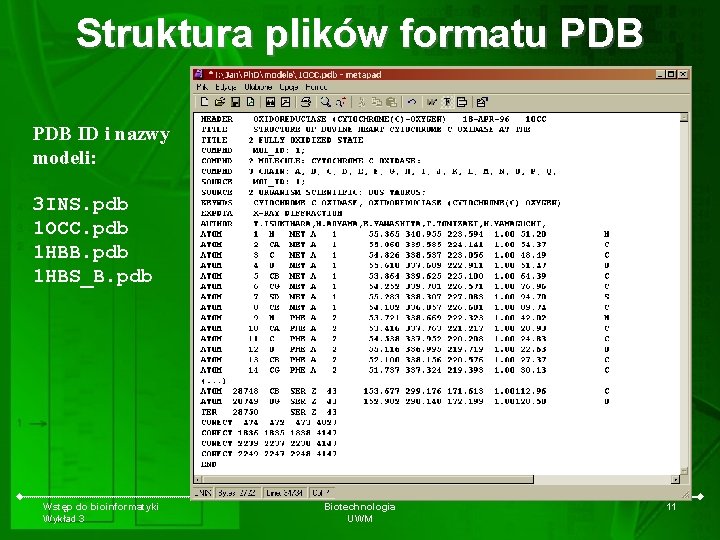
Struktura plików formatu PDB ID i nazwy modeli: 3 INS. pdb 1 OCC. pdb 1 HBB. pdb 1 HBS_B. pdb Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 11

Struktura plików formatu PDB Atom | Grupa | koordynaty Atom nr pierw. aa nr ATOM 1 ATOM 2 ATOM 3 N GLU E 2 CA GLU E 2 C GLU E 2 81. 22 N 79. 85 C 77. 71 C ATOM CE NZ N CA 61. 111 109. 195 71. 915 1. 00 62. 536 109. 629 72. 073 1. 00 62. 684 110. 940 72. 870 1. 00 … 287 40. 779 94. 441 56. 683 1. 00 287 40. 358 93. 365 55. 729 1. 00 288 37. 197 93. 978 55. 486 1. 00 288 36. 979 92. 633 54. 915 1. 00 81. 45 78. 86 89. 74 91. 52 2238 2239 2240 2241 Wstęp do bioinformatyki Wykład 3 LYS ALA E E X Y |inne parametry Biotechnologia UWM Z współcz. rodz 12 C N N C

przewidywanie Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 13

Profil hydrofobowości • • Skale hydrofobowości Analiza pozycji w sekwencji Analiza regionów sekwencji profil Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 14
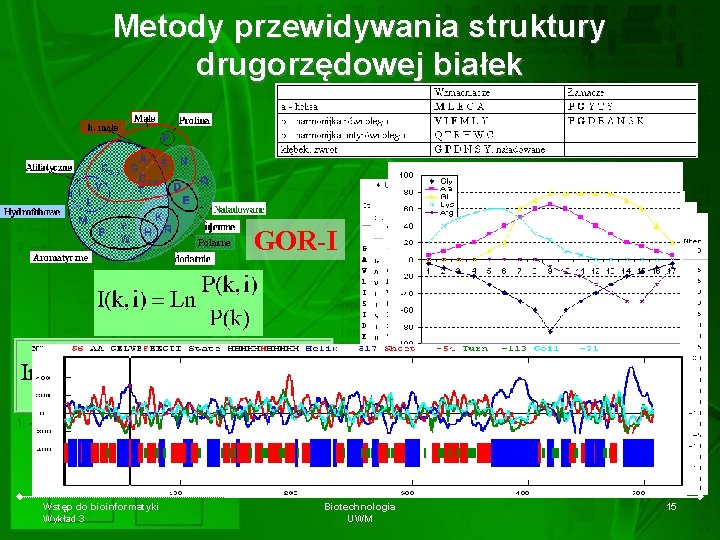
Metody przewidywania struktury drugorzędowej białek GOR-I Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 15
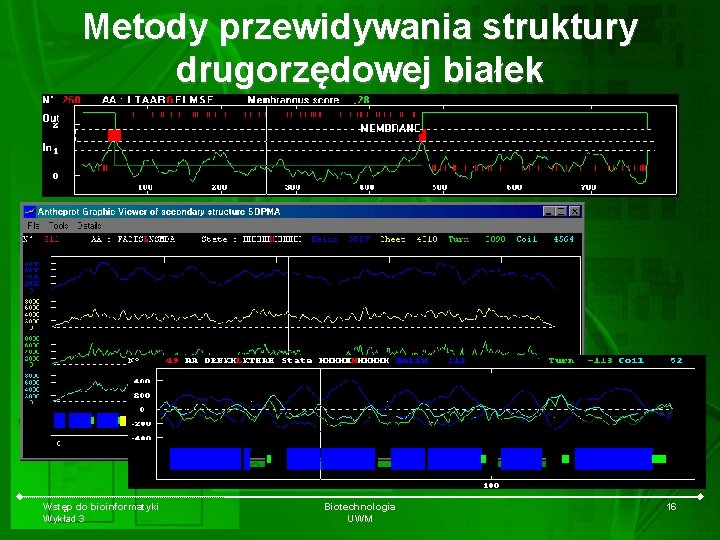
Metody przewidywania struktury drugorzędowej białek GOR-I Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 16
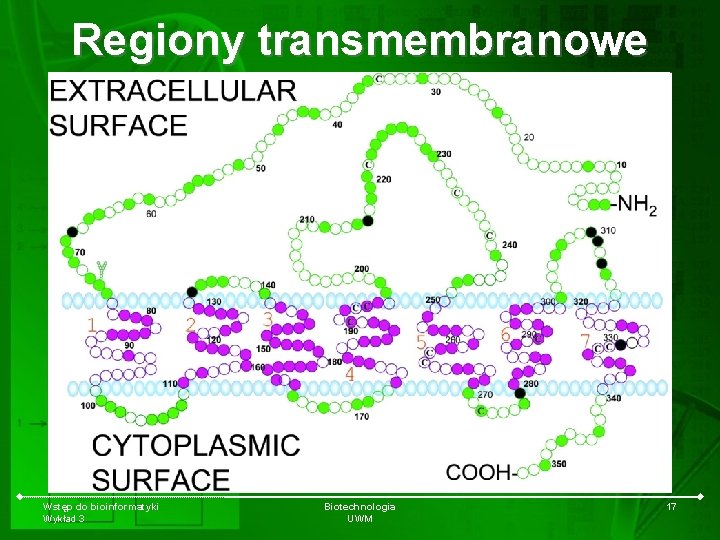
Regiony transmembranowe Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 17

Regiony transmembranowe • The prediction of transmembranous regions is either based on the hydrophobicity method (Kyte & Doolittle, 1982) or on more specific method such as the positive inside rule (Von Heijne, 1992). • The method is based on the positive inside rule that indicates that the cytoplasmic side of a membrane is rather positively charged whereas the external side is rather negatively charged. The hydrophobicvity scale is : Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 18

Regiony transmembranowe • The hydrophobicity of segments is first measured by calculating the weighted sum on a 21 AA trapezoid sliding window with a central, 11 AA rectangular section and 2 flanking wedge-like sections each 5 AA long. The cytoplasmic regions (In) are predicted using the positiveinside rule and the periplasmic regions (Out) of bacterial inner membrane proteins. Thus the formulae is: Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 19
Otrzymywanie modeli struktury białek 1. Metody laboratoryjne – NMR, X-ray 2. Teoretyczne przewidywanie struktury – Ab initio protein modelling – Comparative protein modelling • • modelowanie homologiczne threading (nawlekanie) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 20

NMR Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 21
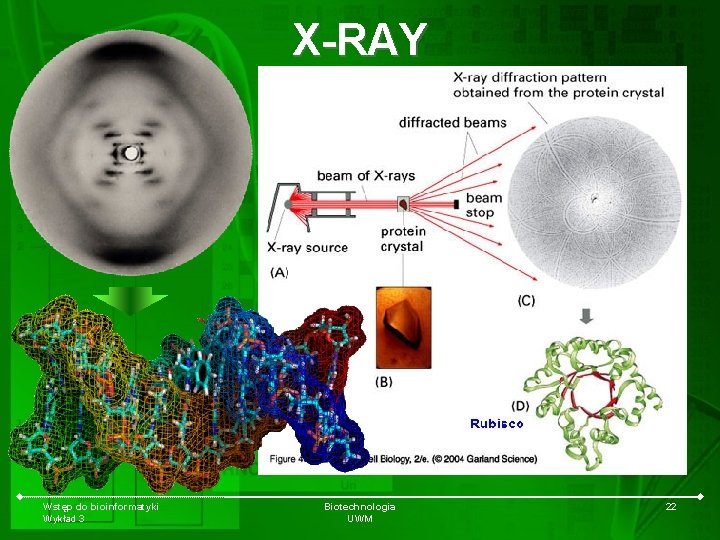
X-RAY Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 22

Metody przewidywania struktury przestrzennej białek in silico 1. Ab initio (de novo) symulacje: - Minimalizacja energii (EM), - dynamika molekularna (MD), - Monte Carlo GHIKLSYTVNEQNLKPERFFYTSAVAIL 2. comparative / homology modeling GHIKLSYTVNEQNLKPERFFYTSAVAIL THEESEQTEN-CESALIGN--NICELY ||| |||||| THE—SEQ-EN-CE-ALIGNEDNICELY Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 23
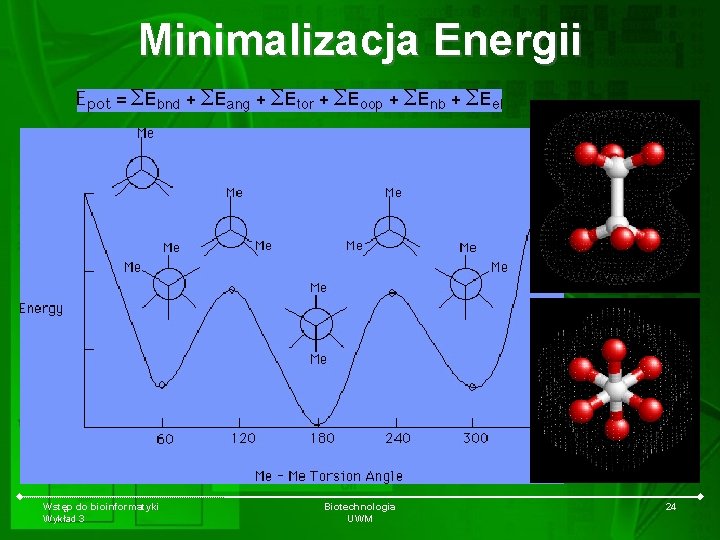
Minimalizacja Energii Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 24
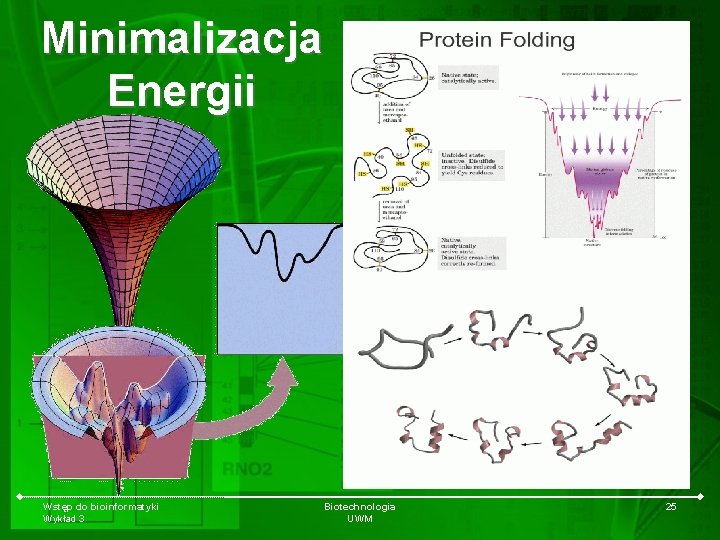
Minimalizacja Energii Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 25
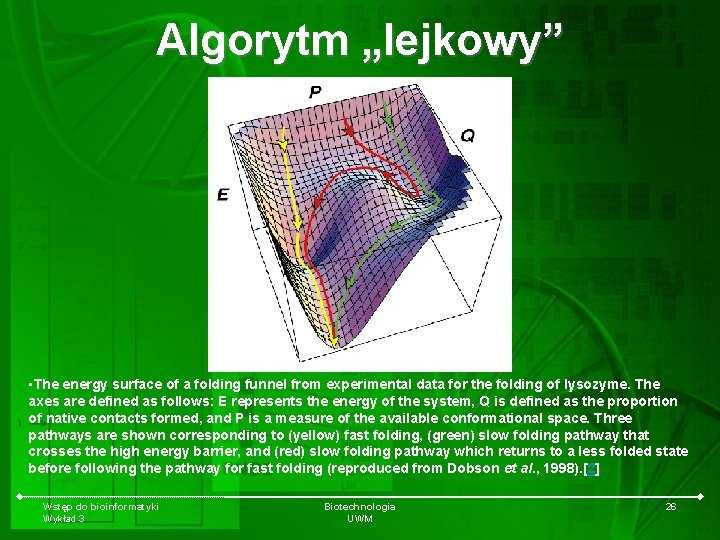
Algorytm „lejkowy” • The energy surface of a folding funnel from experimental data for the folding of lysozyme. The axes are defined as follows: E represents the energy of the system, Q is defined as the proportion of native contacts formed, and P is a measure of the available conformational space. Three pathways are shown corresponding to (yellow) fast folding, (green) slow folding pathway that crosses the high energy barrier, and (red) slow folding pathway which returns to a less folded state before following the pathway for fast folding (reproduced from Dobson et al. , 1998). [2] Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 26
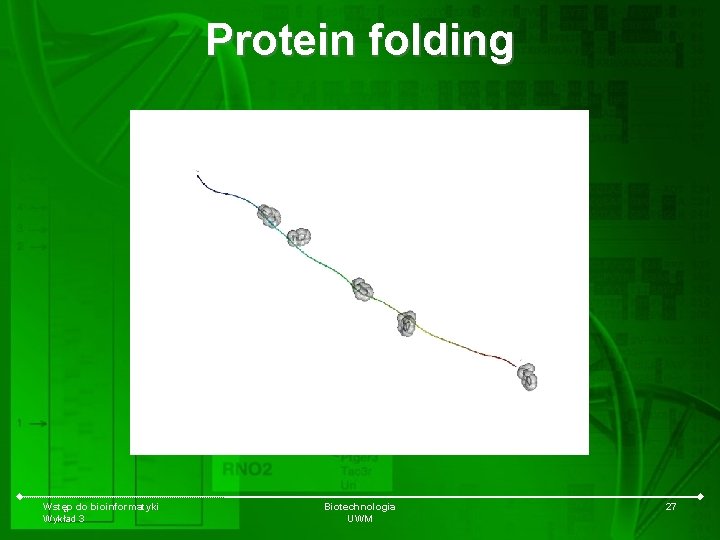
Protein folding Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 27
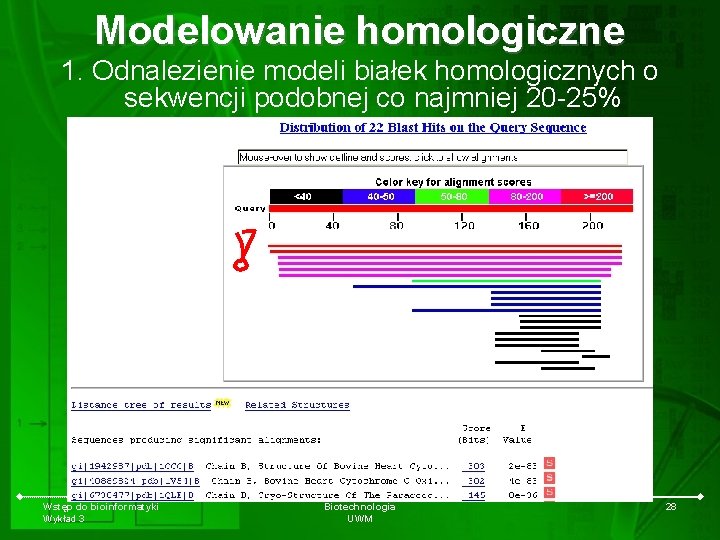
Modelowanie homologiczne 1. Odnalezienie modeli białek homologicznych o sekwencji podobnej co najmniej 20 -25% Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 28
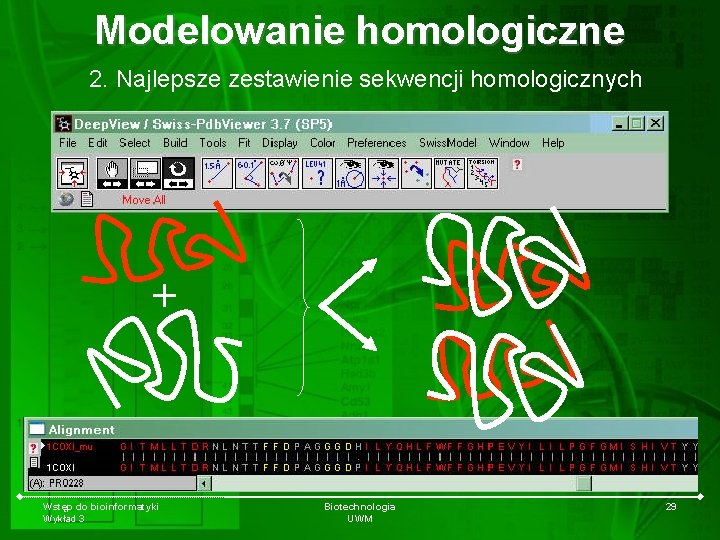
Modelowanie homologiczne 2. Najlepsze zestawienie sekwencji homologicznych + Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 29
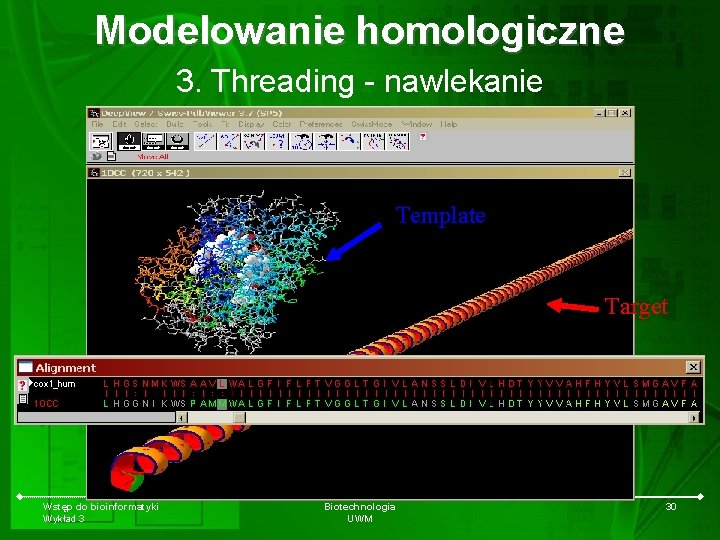
Modelowanie homologiczne 3. Threading - nawlekanie Template Target Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 30

Modelowanie homologiczne 4. Optymalizacja modelu / projektu Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 31

wizualizacja Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 32

Podstawowe elementy w wizualizacji molekularnej Punkty i linie (druty) (points and wires) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 33

Podstawowe elementy w wizualizacji molekularnej Kule i pręty (słomki, rurki) (balls and sticks) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 34
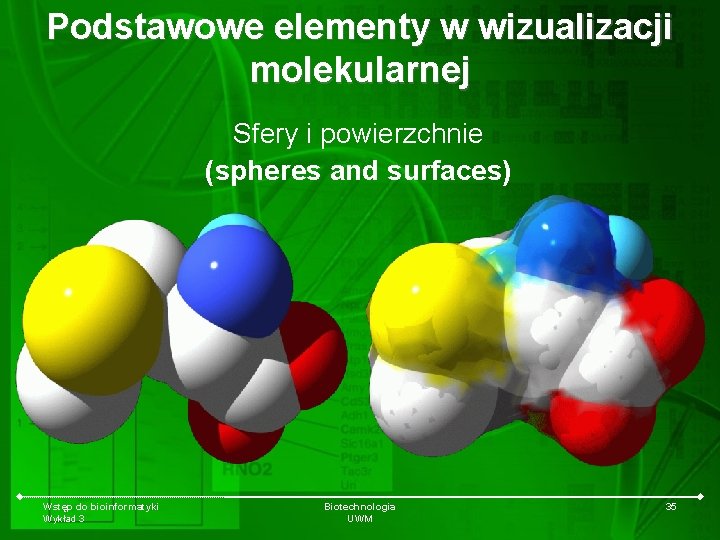
Podstawowe elementy w wizualizacji molekularnej Sfery i powierzchnie (spheres and surfaces) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 35
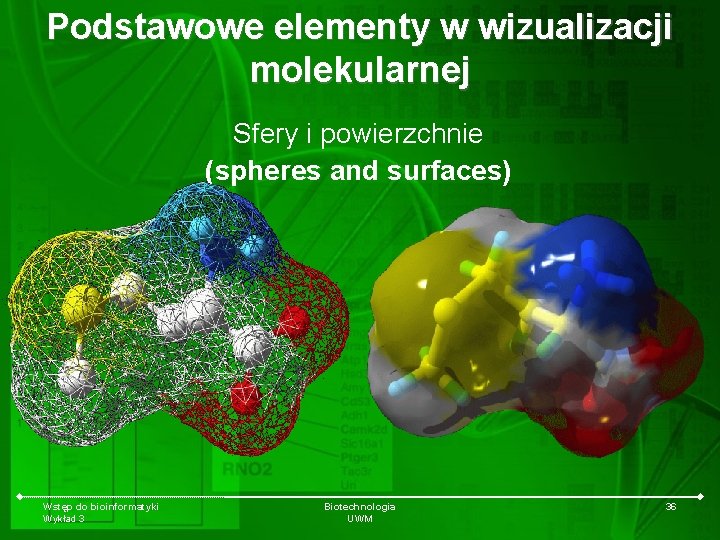
Podstawowe elementy w wizualizacji molekularnej Sfery i powierzchnie (spheres and surfaces) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 36
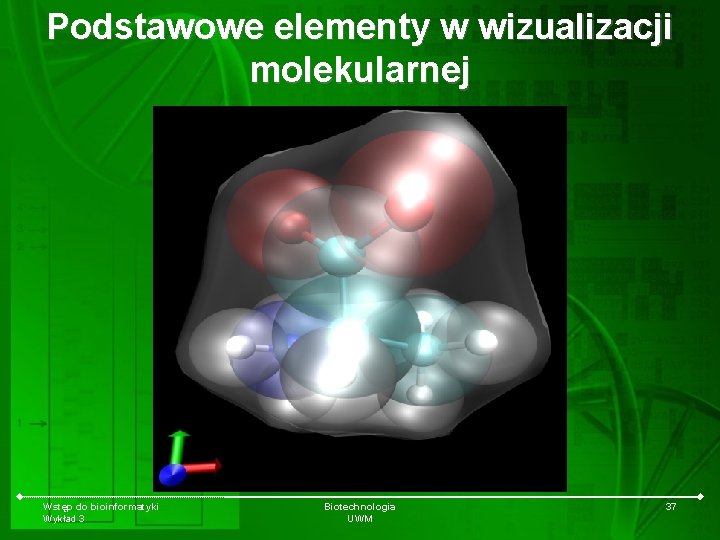
Podstawowe elementy w wizualizacji molekularnej Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 37

Podstawowe elementy w wizualizacji molekularnej Wstążki i nici (ribbons and coils) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 38
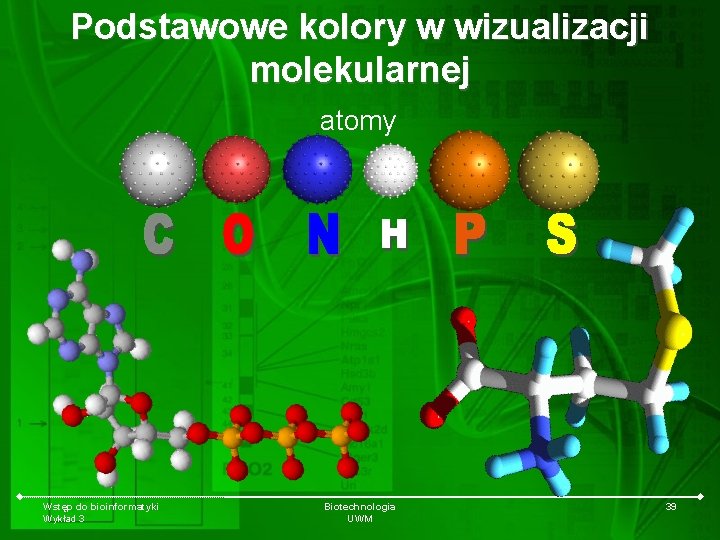
Podstawowe kolory w wizualizacji molekularnej atomy Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 39
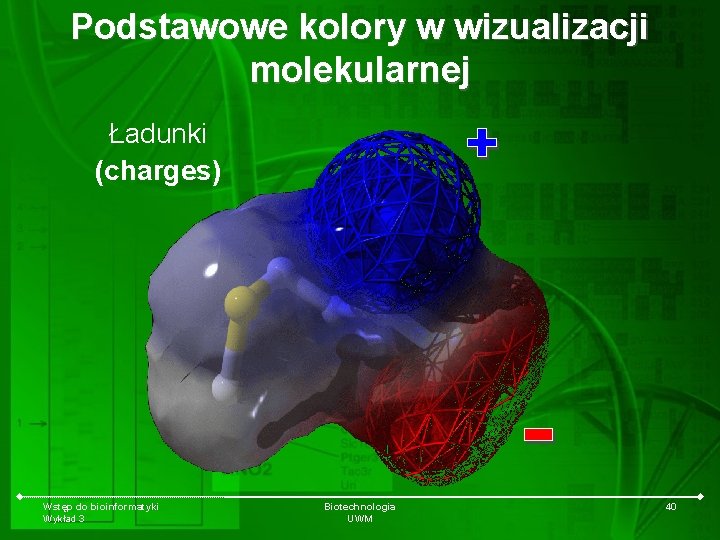
Podstawowe kolory w wizualizacji molekularnej Ładunki (charges) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 40

Podstawowe typy wizualizacji molekularnej wireframe (obraz szkieletowy) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 41
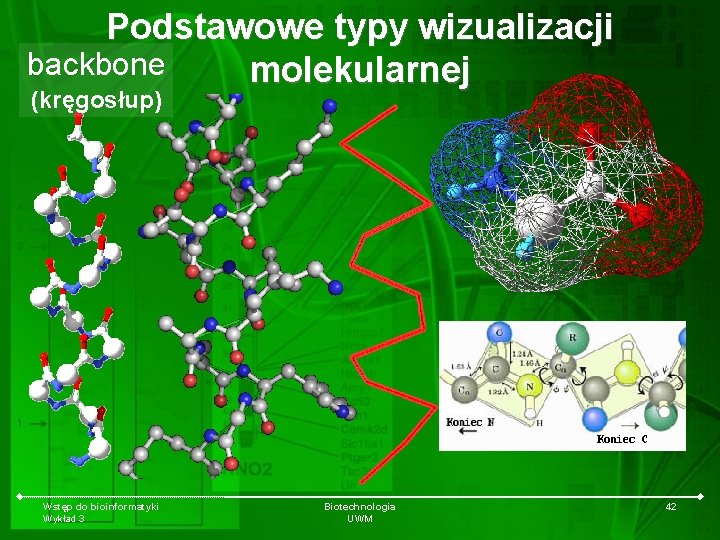
Podstawowe typy wizualizacji backbone molekularnej (kręgosłup) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 42
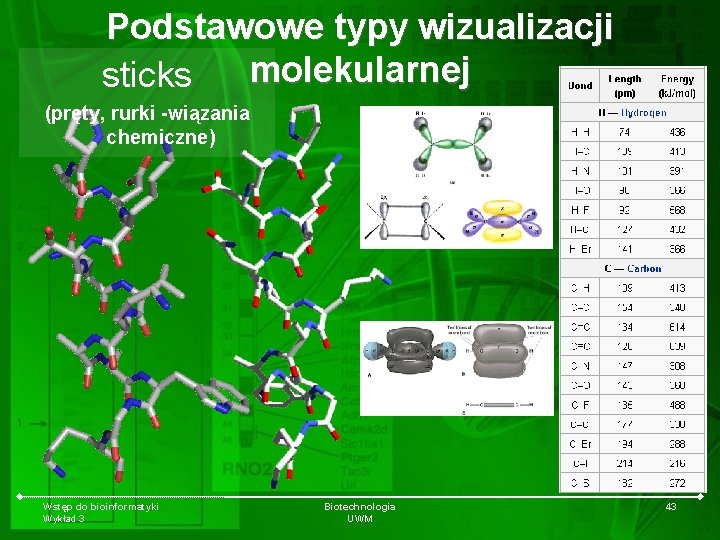
Podstawowe typy wizualizacji molekularnej sticks (pręty, rurki -wiązania chemiczne) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 43
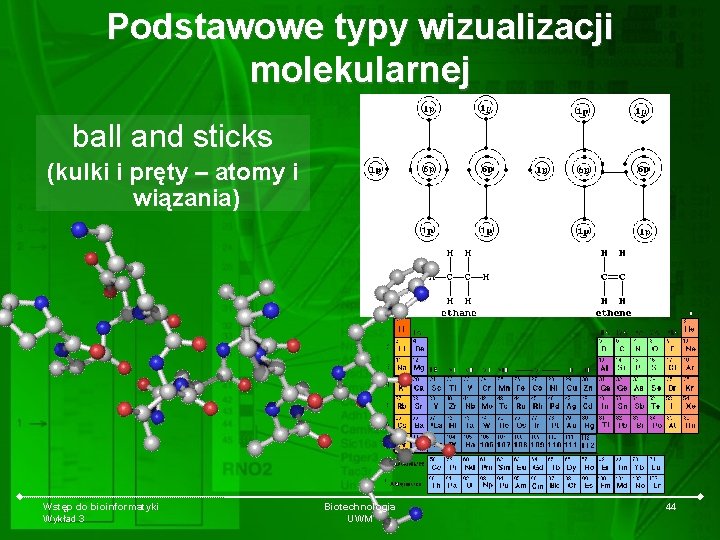
Podstawowe typy wizualizacji molekularnej ball and sticks (kulki i pręty – atomy i wiązania) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 44

Podstawowe typy wizualizacji molekularnej ribbons i cartoon (wstążki – wzajemne ułożenie powierzchni wiązań peptydowych) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 45

Podstawowe typy wizualizacji molekularnej wstążki Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 46
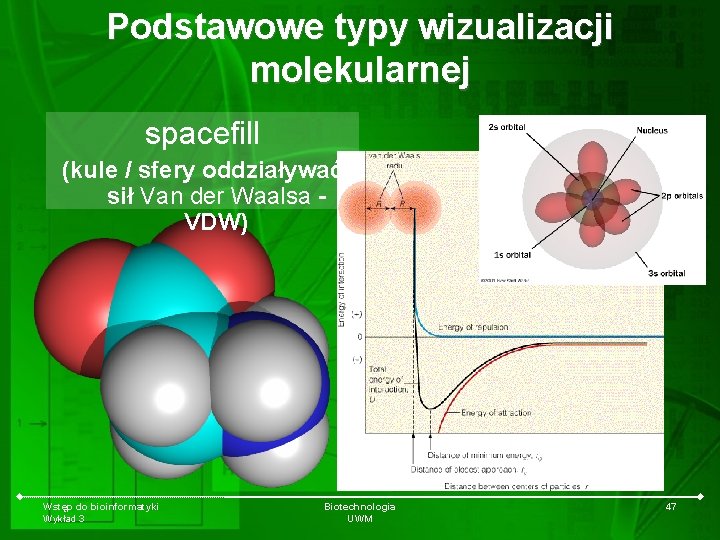
Podstawowe typy wizualizacji molekularnej spacefill (kule / sfery oddziaływać sił Van der Waalsa VDW) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 47
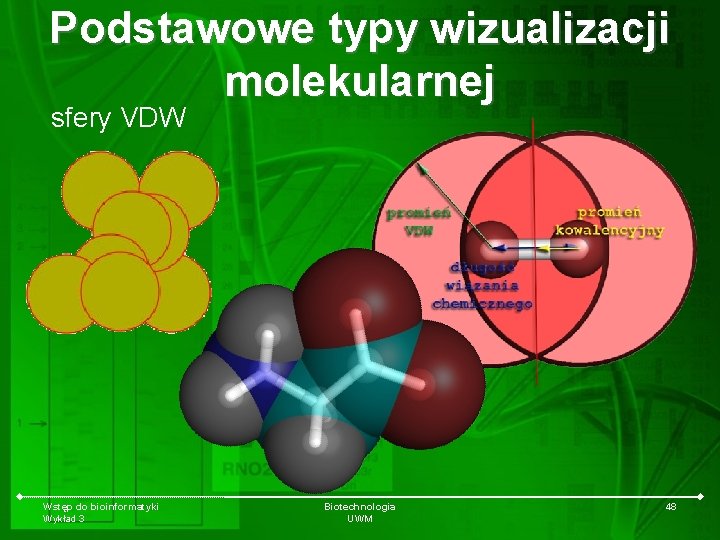
Podstawowe typy wizualizacji molekularnej sfery VDW Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 48
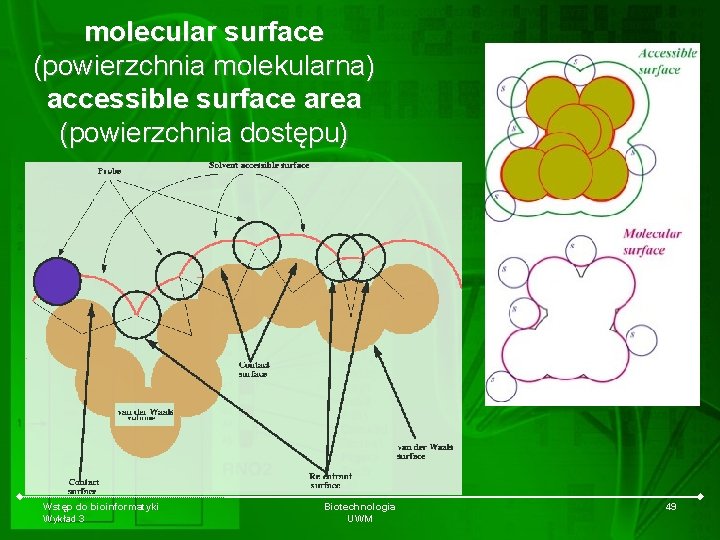
molecular surface (powierzchnia molekularna) accessible surface area (powierzchnia dostępu) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 49
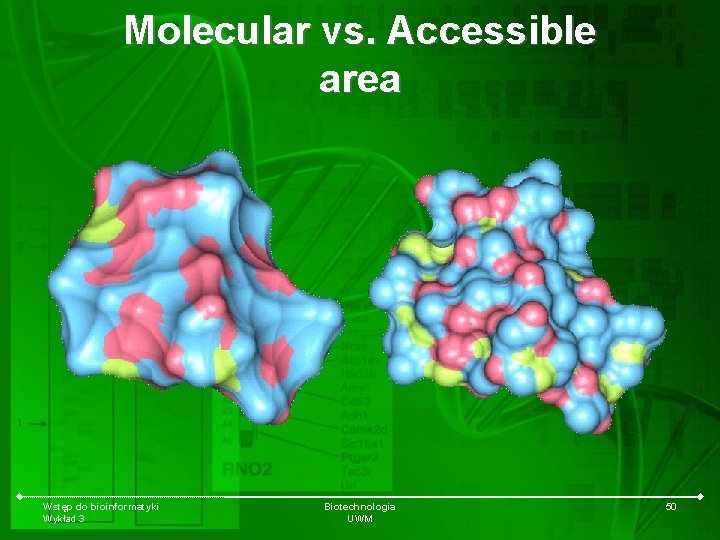
Molecular vs. Accessible area Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 50

Podstawowe typy wizualizacji molekularnej molecular surface (powierzchnia molekularna) accessible surface area (powierzchnia dostępu) electrostatic surface area (powierzchnia elektrostatyczna) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 51
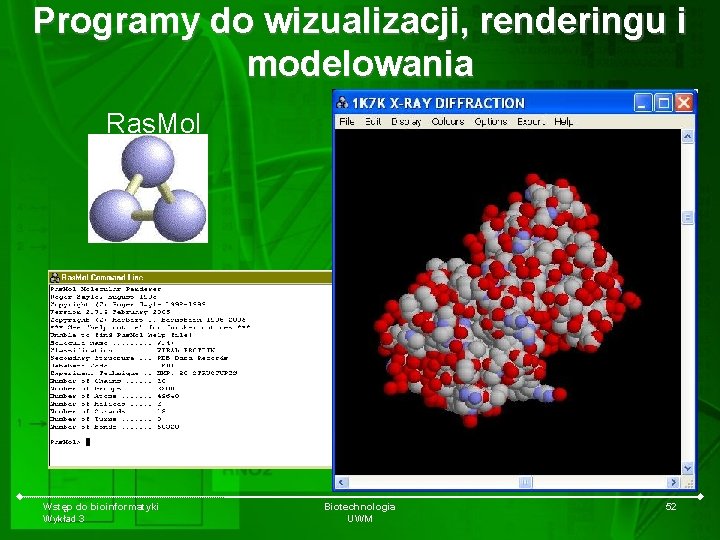
Programy do wizualizacji, renderingu i modelowania Ras. Mol Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 52
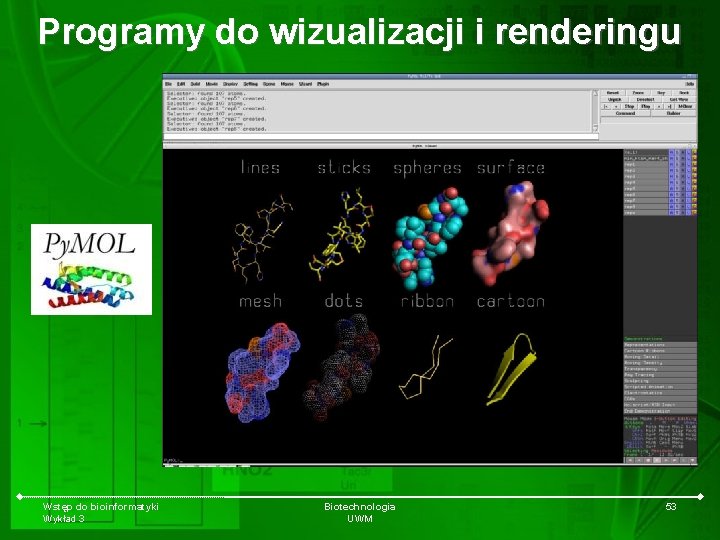
Programy do wizualizacji i renderingu Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 53
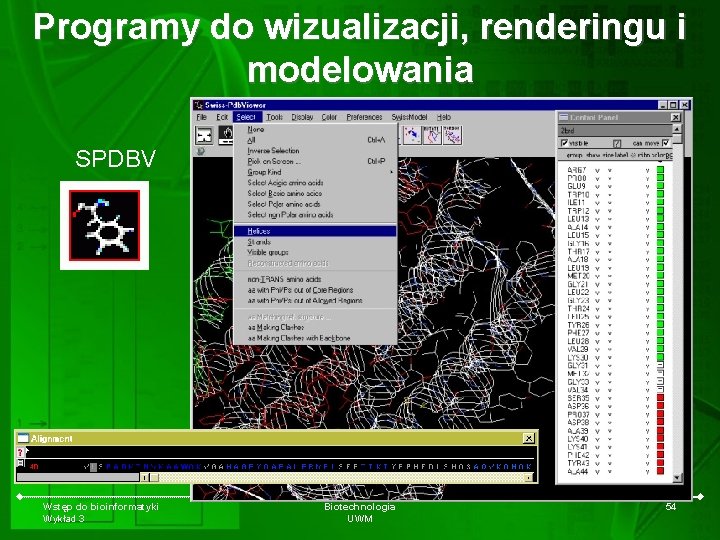
Programy do wizualizacji, renderingu i modelowania SPDBV Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 54
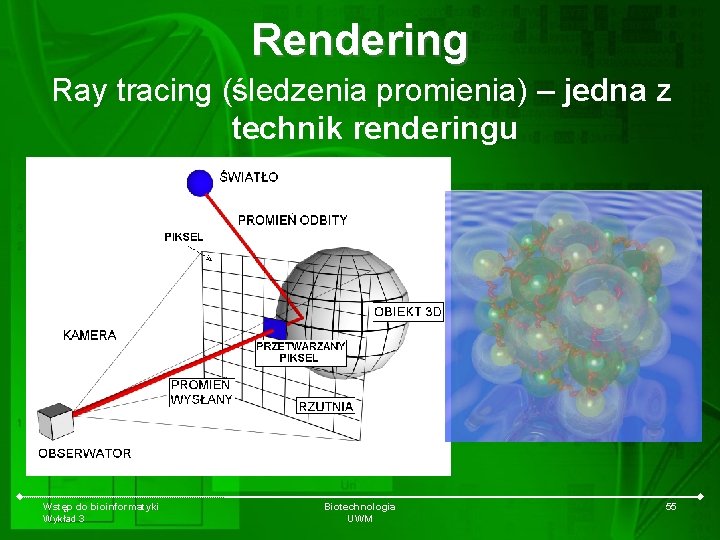
Rendering Ray tracing (śledzenia promienia) – jedna z technik renderingu Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 55

Programy do wizualizacji i renderingu Pov. Ray Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 56
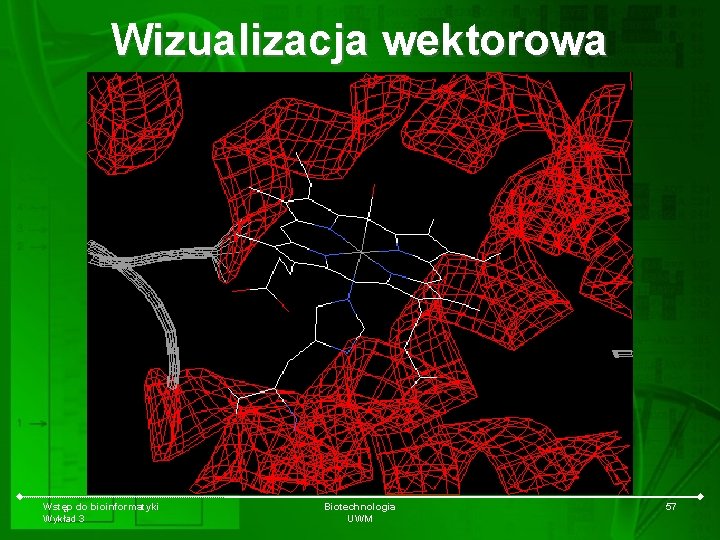
Wizualizacja wektorowa Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 57
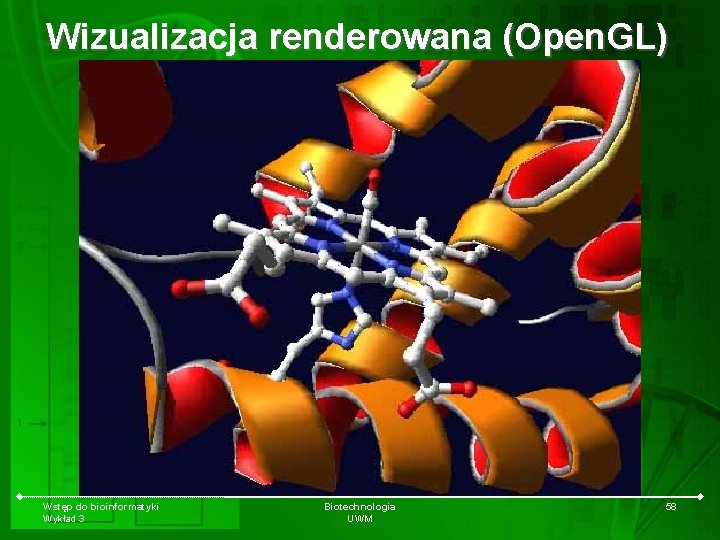
Wizualizacja renderowana (Open. GL) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 58
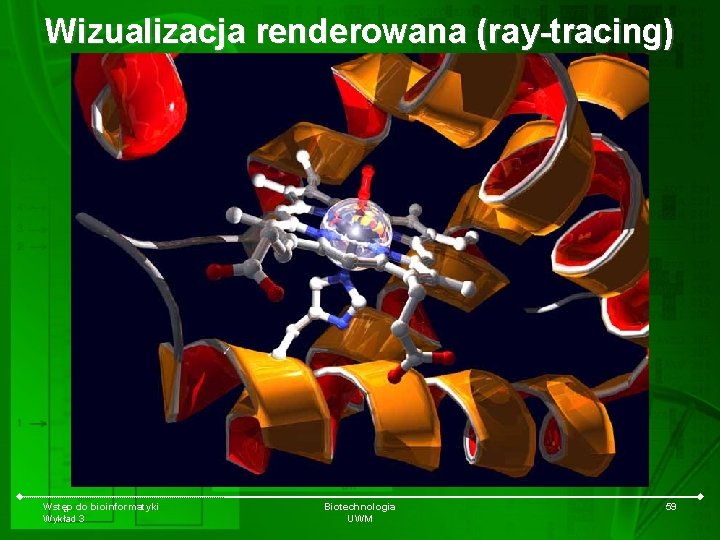
Wizualizacja renderowana (ray-tracing) Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 59

Ray-tracing Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 60
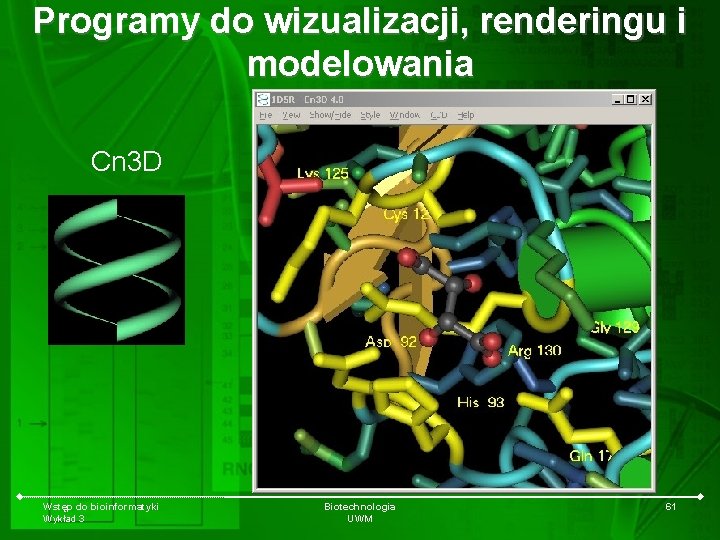
Programy do wizualizacji, renderingu i modelowania Cn 3 D Wstęp do bioinformatyki Wykład 3 Biotechnologia UWM 61
- Slides: 61