Squenage dune rgion cible en relation avec le

Séquençage d’une région ciblée en relation avec le développement musculaire dans la race bovine Limousine. Colloque ATC 2017
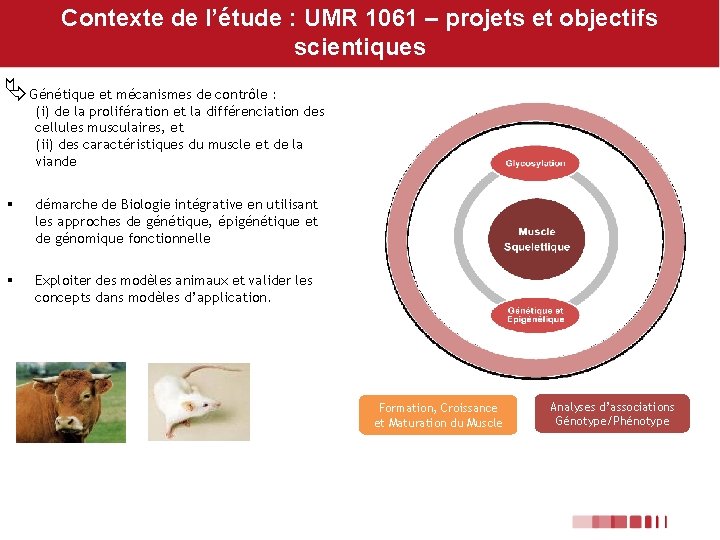
Contexte de l’étude : UMR 1061 – projets et objectifs scientiques Génétique et mécanismes de contrôle : (i) de la prolifération et la différenciation des cellules musculaires, et (ii) des caractéristiques du muscle et de la viande § démarche de Biologie intégrative en utilisant les approches de génétique, épigénétique et de génomique fonctionnelle § Exploiter des modèles animaux et valider les concepts dans modèles d’application. Formation, Croissance et Maturation du Muscle Analyses d’associations Génotype/Phénotype
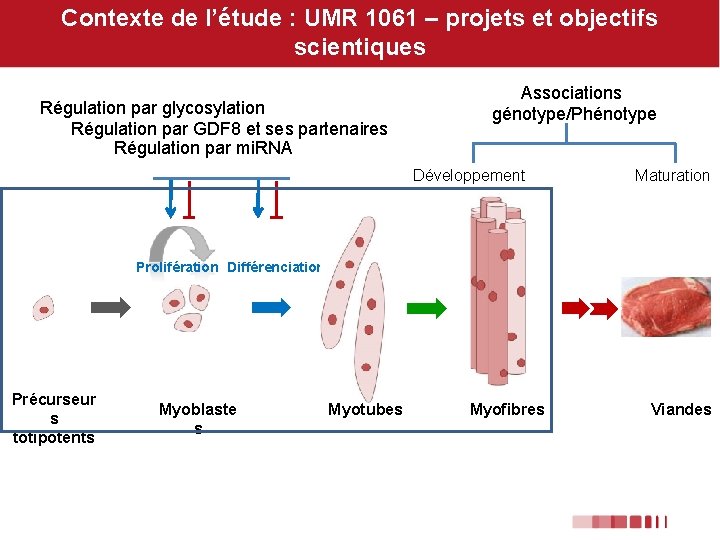
Contexte de l’étude : UMR 1061 – projets et objectifs scientiques Régulation par glycosylation Régulation par GDF 8 et ses partenaires Régulation par mi. RNA Associations génotype/Phénotype Développement Maturation Prolifération Différenciation Précurseur s totipotents Myoblaste s Myotubes Myofibres Viandes
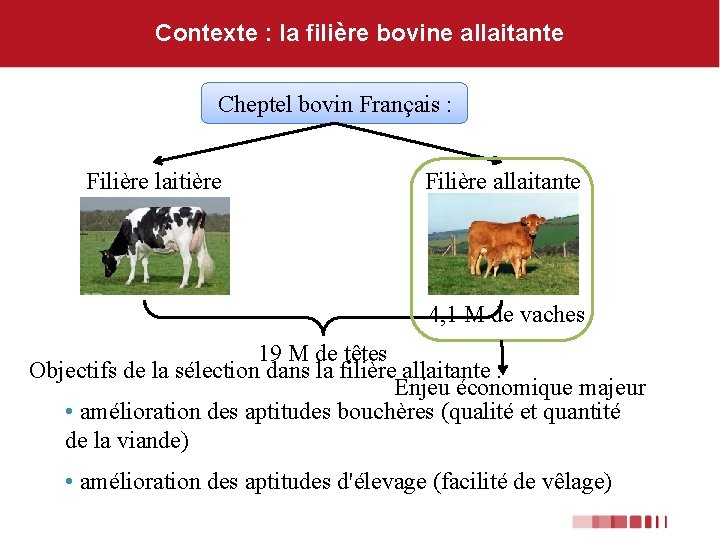
Contexte : la filière bovine allaitante Cheptel bovin Français : Filière laitière Filière allaitante 4, 1 M de vaches 19 M de têtes Objectifs de la sélection dans la filière allaitante : Enjeu économique majeur • amélioration des aptitudes bouchères (qualité et quantité de la viande) • amélioration des aptitudes d'élevage (facilité de vêlage)
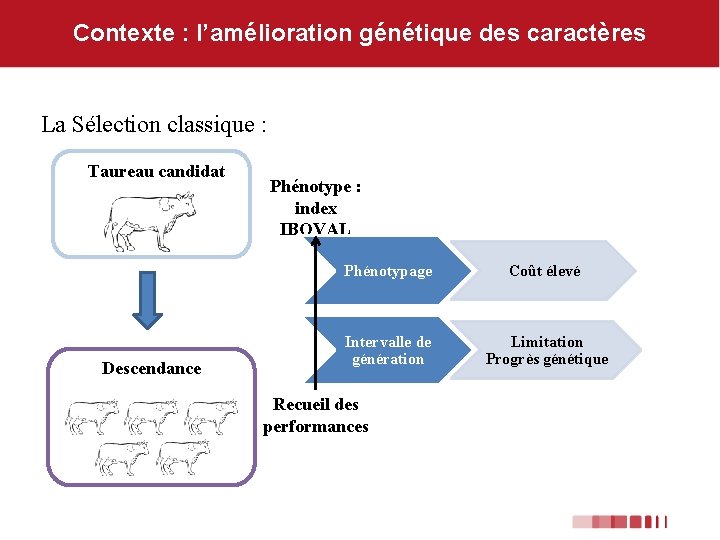
Contexte : l’amélioration génétique des caractères La Sélection classique : Taureau candidat Descendance Phénotype : index IBOVAL Phénotypage Coût élevé Intervalle de génération Limitation Progrès génétique Recueil des performances
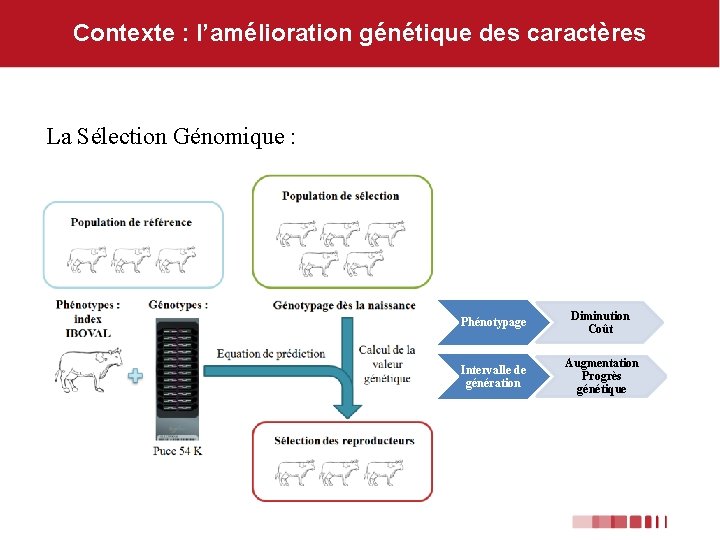
Contexte : l’amélioration génétique des caractères La Sélection Génomique : Phénotypage Diminution Coût Intervalle de génération Augmentation Progrès génétique
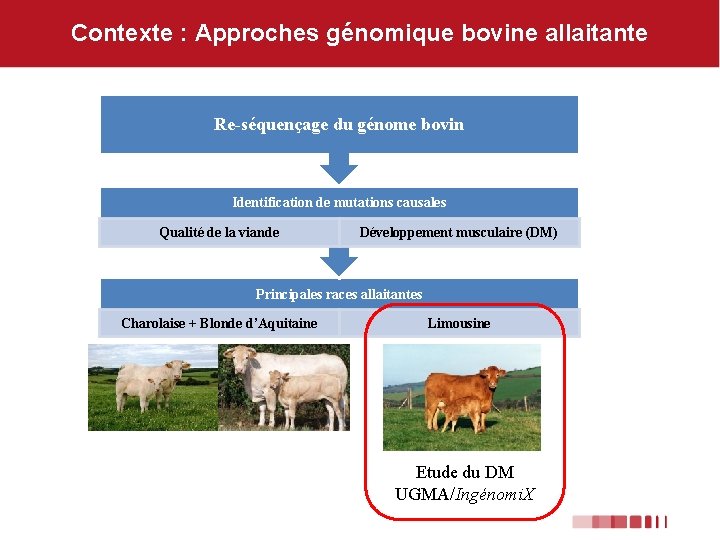
Contexte : Approches génomique bovine allaitante Re-séquençage du génome bovin Identification de mutations causales Qualité de la viande Développement musculaire (DM) Principales races allaitantes Charolaise + Blonde d’Aquitaine Limousine Etude du DM UGMA/Ingénomi. X

Contexte : La région d’intérêt • Etudes d’association : région de 4, 439 Mb, située un Chr. Aut. : 4 500 000 -8 939 028 fortement associée au DM • 19 gènes, 2 pseudogènes et 5 mi-ARN
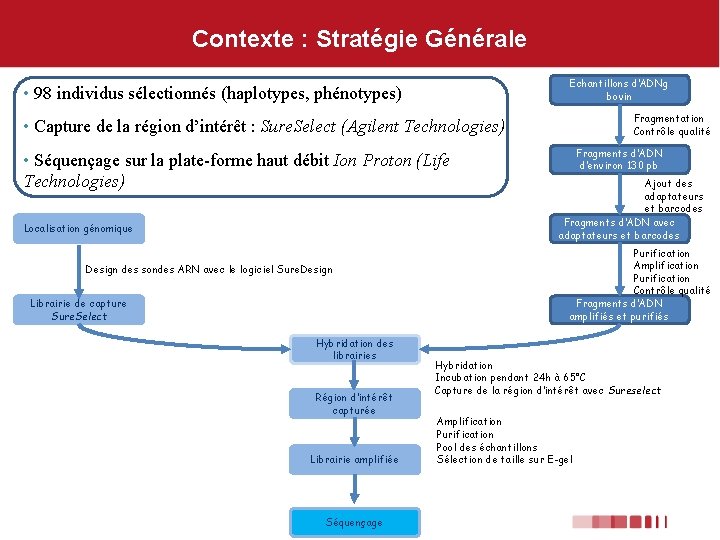
Contexte : Stratégie Générale Echantillons d’ADNg bovin • 98 individus sélectionnés (haplotypes, phénotypes) Fragmentation Contrôle qualité • Capture de la région d’intérêt : Sure. Select (Agilent Technologies) • Séquençage sur la plate-forme haut débit Ion Proton (Life Technologies) Localisation génomique Design des sondes ARN avec le logiciel Sure. Design Librairie de capture Sure. Select Hybridation des librairies Région d’intérêt capturée Librairie amplifiée Séquençage Fragments d’ADN d’environ 130 pb Ajout des adaptateurs et barcodes Fragments d’ADN avec adaptateurs et barcodes Purification Amplification Purification Contrôle qualité Fragments d’ADN amplifiés et purifiés Hybridation Incubation pendant 24 h à 65°C Capture de la région d’intérêt avec Sureselect Amplification Purification Pool des échantillons Sélection de taille sur E-gel

Protocole : Le design des sondes • Capture grâce à 55 497 sondes (2 X) • Presque 100 % des régions codantes couvertes • Capture totale théorique : 68, 5 % de la région d’intérêt
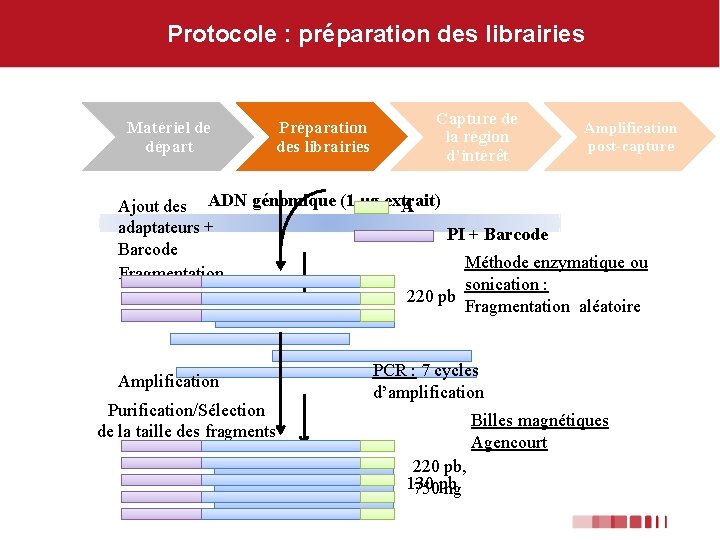
Protocole : préparation des librairies Matériel de départ Préparation des librairies Capture de la région d’intérêt Amplification post-capture Ajout des ADN génomique (1 µg extrait) A adaptateurs + PI + Barcode Méthode enzymatique ou Fragmentation sonication : 220 pb Fragmentation aléatoire Amplification Purification/Sélection de la taille des fragments PCR : 7 cycles d’amplification Billes magnétiques Agencourt 220 pb, 130 750 pb ng
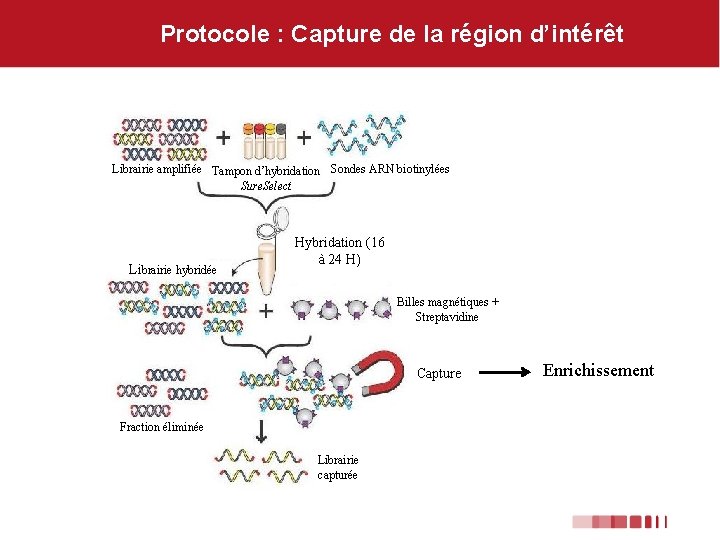
Protocole : Capture de la région d’intérêt Librairie amplifiée Tampon d’hybridation Sondes ARN biotinylées Sure. Select Librairie hybridée Hybridation (16 à 24 H) Billes magnétiques + Streptavidine Capture Fraction éliminée Librairie capturée Enrichissement
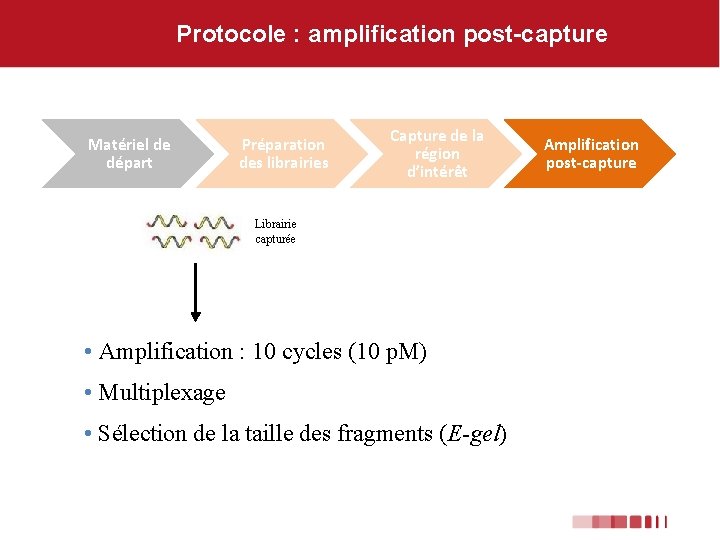
Protocole : amplification post-capture Matériel de départ Préparation des librairies Capture de la région d’intérêt Librairie capturée • Amplification : 10 cycles (10 p. M) • Multiplexage • Sélection de la taille des fragments (E-gel) Amplification post-capture
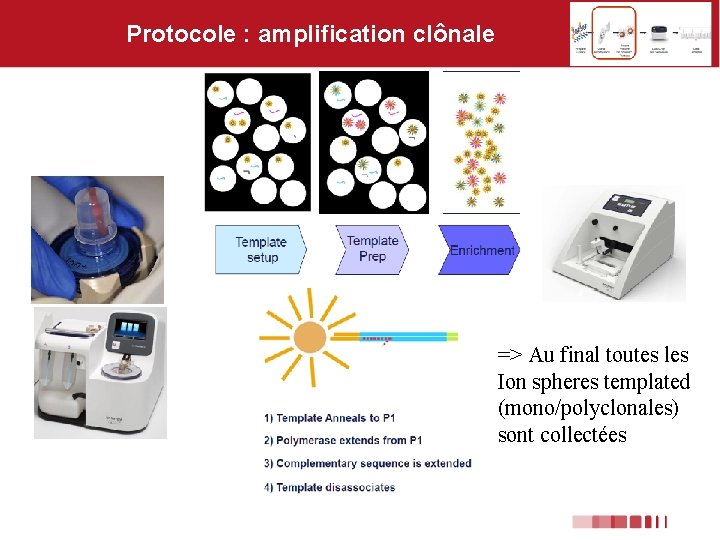
Protocole : amplification clônale => Au final toutes les Ion spheres templated (mono/polyclonales) sont collectées
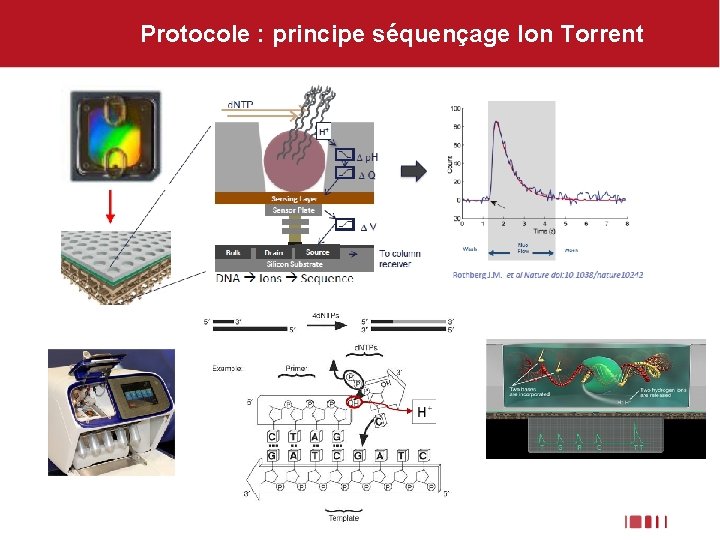
Protocole : principe séquençage Ion Torrent
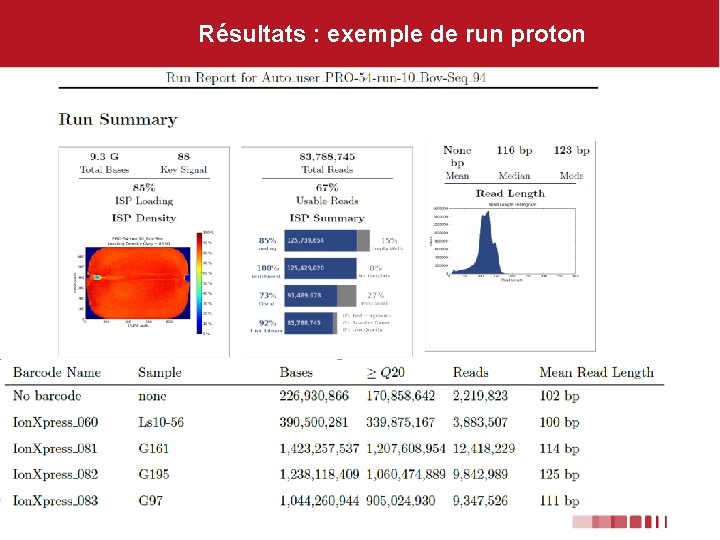
Résultats : exemple de run proton

Résultats quantitatifs 98 échantillons séquençés en 12 runs (multiplexage X 8 et X 10): • ~9, 5 M des reads/éch (~125 pb) • 99 % des « reads » mappées sur génome bovin mais : • 24 % de duplicats de PCR • 25 % des reads sur région cible ~57 % de la région-cible séquencée (20 X) • 92% des régions codantes (20 X) Au final, 7072 variations détectées (6465 SNPs et 607 Indels)
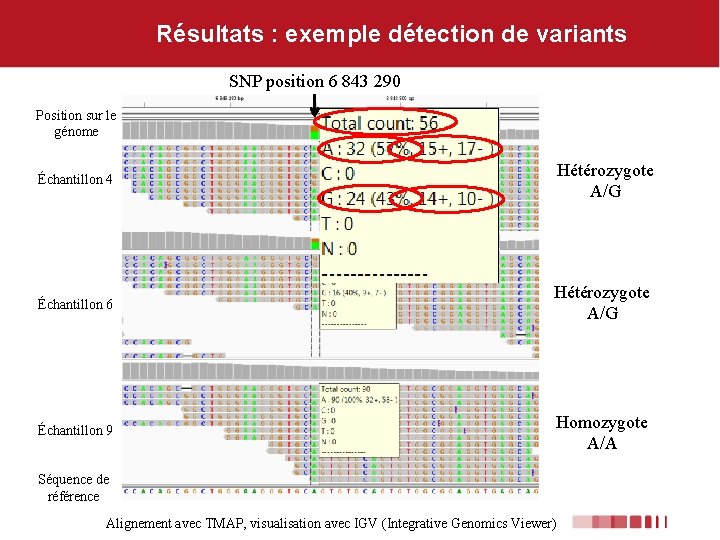
Résultats : exemple détection de variants SNP position 6 843 290 Position sur le génome Échantillon 4 Hétérozygote A/G Échantillon 6 Hétérozygote A/G Échantillon 9 Homozygote A/A Séquence de référence Alignement avec TMAP, visualisation avec IGV (Integrative Genomics Viewer)
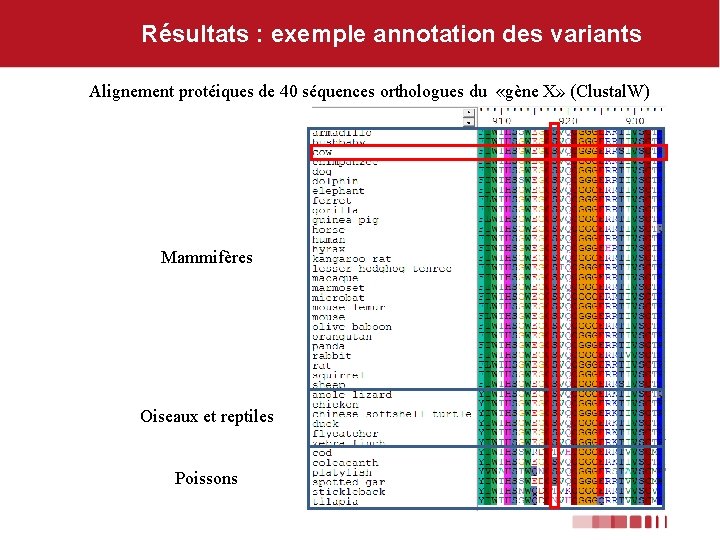
Résultats : exemple annotation des variants Alignement protéiques de 40 séquences orthologues du «gène X» (Clustal. W) Mammifères Oiseaux et reptiles Poissons
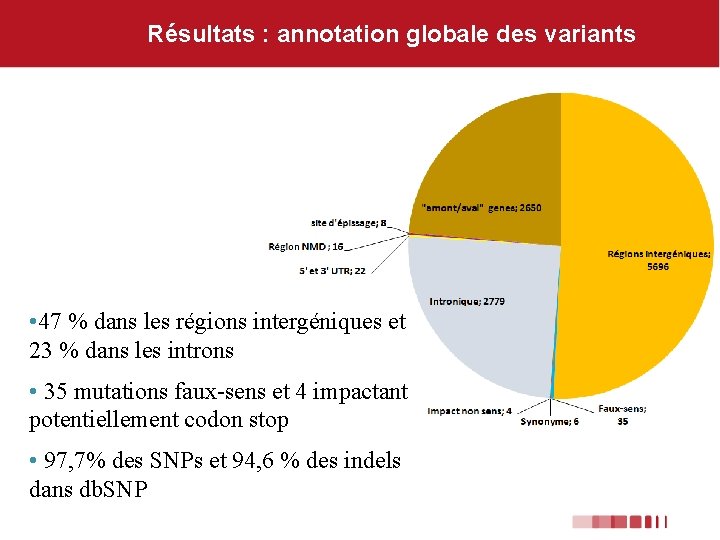
Résultats : annotation globale des variants • 47 % dans les régions intergéniques et 23 % dans les introns • 35 mutations faux-sens et 4 impactant potentiellement codon stop • 97, 7% des SNPs et 94, 6 % des indels dans db. SNP

Conclusions • Validation stratégie et approche technologique (optimisation multiplexage, profondeur séquençage satisfaisante) • Enrichissement très convenable : ~4640 SNPs et 307 indels détectés par échantillon • Niveau d’analyse des séquences codantes optimum, plus contrasté sur séquences introniques et surtout intergéniques (intérêt ? Probléme des séquences répétées)

Perspectives • Confirmation détection et annotation des variants • Analyses de concordance génotype/phénotype : sélection de(s) variant(s) d’intérêt • => identification de mutation(s) causale(s) • Génotypage sur l’ensemble de la population de référence • => validation variant(s) d’intérêt/mutation(s) causale(s) Intégration dans plan de sélection chez la race limousine ( Amélioration rendement de production viande)

Remerciements Romain Philippe Nathalie Duprat Gabrielle Delpy Véronique Blanquet Sébastien Arico Gaylord Auvray Marc Gambarotto Emilie Guérin Rémy Moulinas

Merci de votre attention
- Slides: 24