Sequenciamento de DNA em Mega BACE DNA Analysis

Sequenciamento de DNA em Mega. BACE DNA Analysis Systems • Prof. Dr. Luciano da Silva Pinto ls_pinto@hotmail. com TGTGAACACACGTGTGGATTGG. . .

Sequenciamento do DNA Definição Identificação da ordem exata dos pares de bases (A, T, G e C) em um segmento de DNA. Importância O conhecimento da seqüência de bases de um gene fornece importantes informações sobre sua estrutura, função e relação evolutiva com outros genes (de um mesmo organismo ou de organismos diferentes).


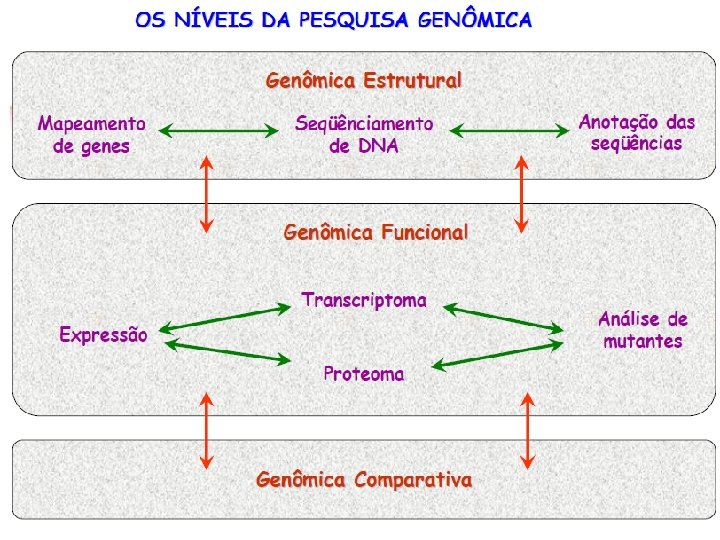
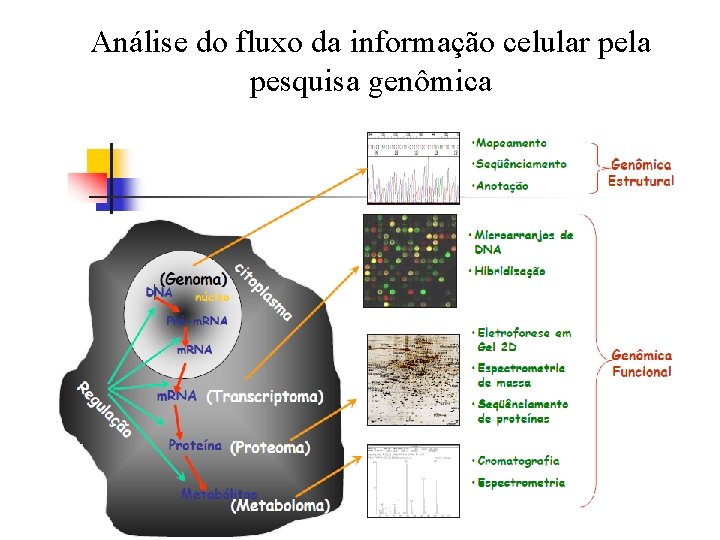
Análise do fluxo da informação celular pela pesquisa genômica
Histórico – O sequenciamento de DNA no tempo Watson & Crick Nobel 1962

Histórico – O sequenciamento de DNA no tempo Frederick Sanger Prêmio Nobel de medicina e fisiologia em 1980 J. Mol. Biol. v. 94, p. 441 -448, 1975 Walter Gilbert Prêmio Nobel de medicina e fisiologia em 1980 PNAS, vol. 74 No. 2 p. 560 -564, 1977
Seqüenciamento de DNA Projeto Genoma Humano

Tecnologias de sequenciamento - Maxam & Gilbert, método químico- 1972 - Sanger sequencing - PNAS 74 (1977), n. 12, 5463 -5467 - Sequenciador Mega. BACE (1 Mpb/24 horas) - Pirosequenciamento - Science 281 (1998), n. 5375, 363 -365 - Nature 437 (2005), 362 -7 - Sequenciador 454 (150 Mpb/24 horas)

Método de Sanger • Reação de seqüenciamento – amplificação linear • Eletroforese em gel de acrilamida – em placa – capilar • Leitura da seqüencia – manual – automática
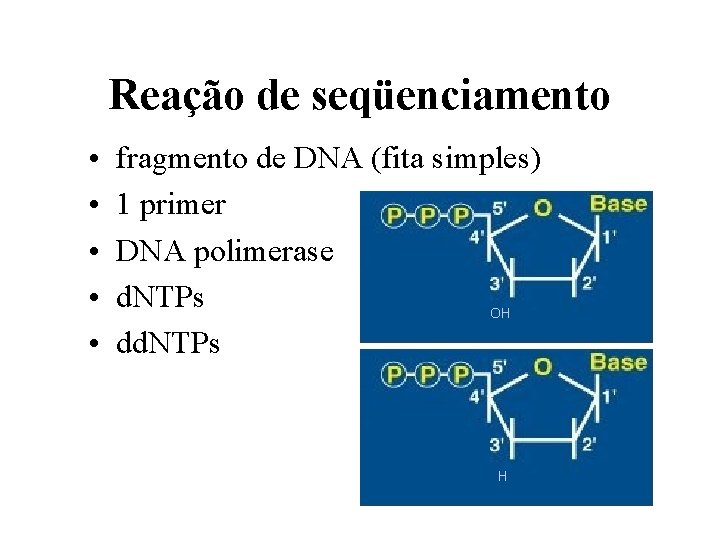
Reação de seqüenciamento • • • fragmento de DNA (fita simples) 1 primer DNA polimerase d. NTPs OH dd. NTPs H
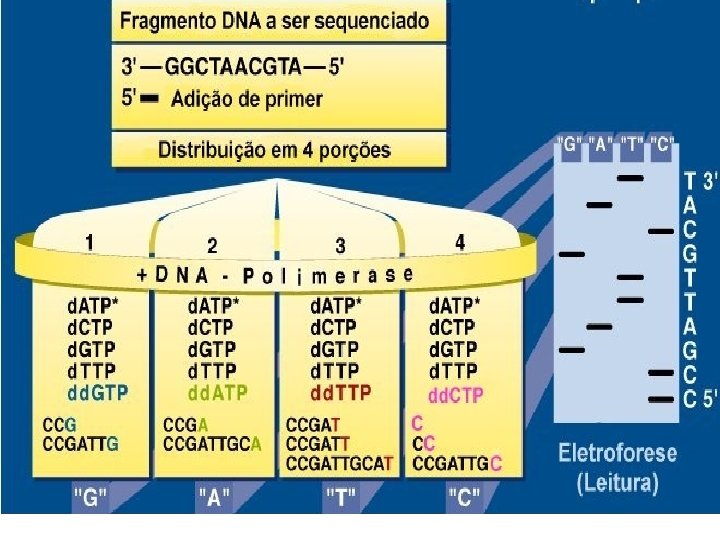

Eletroforese • em placa • capilar

Reação de sequenciamento e marcação do DNA Leitura das sequências Manual Radioisótopos Leitura das sequências Automática Fluoresceínas
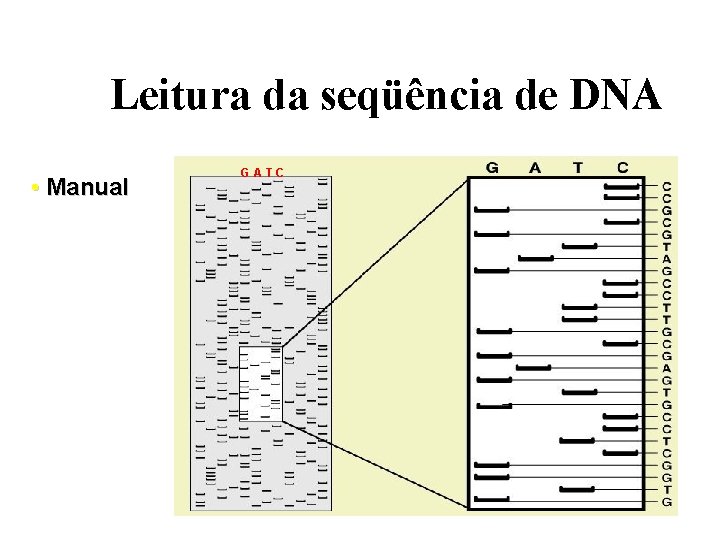
Leitura da seqüência de DNA • Manual GATC
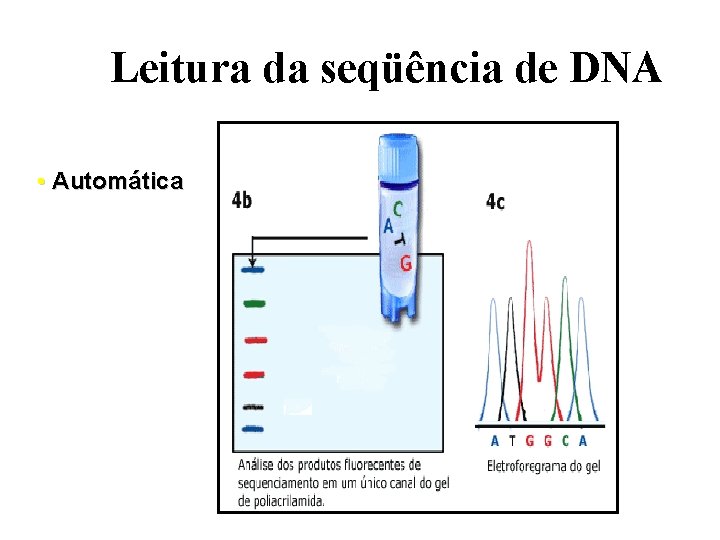
Leitura da seqüência de DNA • Automática
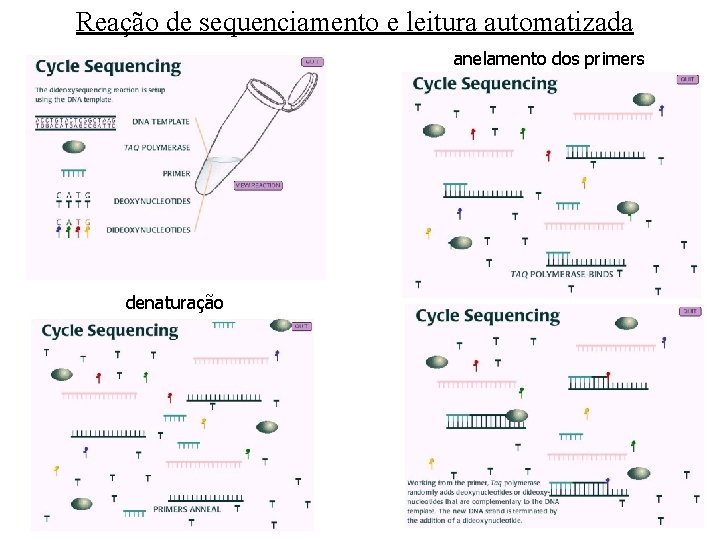
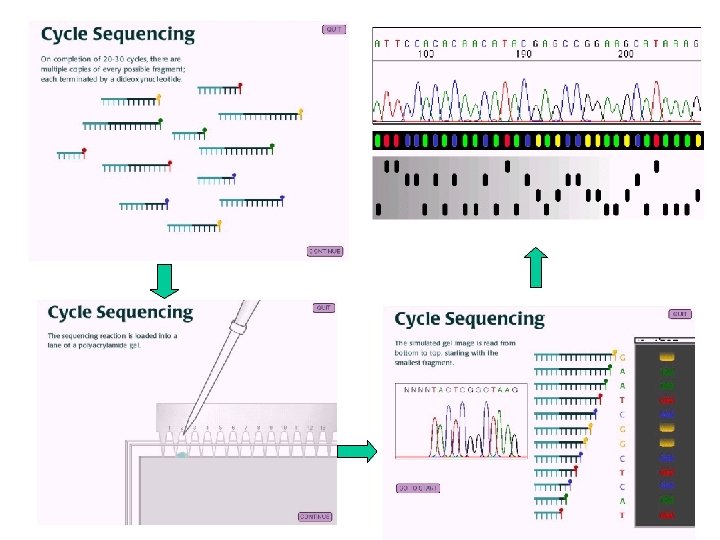
Reação de sequenciamento e leitura automatizada anelamento dos primers denaturação

Organizando as Seqüências de DNA 5’ ATGCTTCTGGCAGATCTGAACAGTGTTACTGATATTGCTT ATGCTTCTGGCAGATCTGAACAGTGTTACTGATAT ATGCTTCTGGCAGATCTGAACAGTGTTACTGATATTGCT ATGCTTCTGGCAGATCTGAACAGTGTTACTGATATT ATGCTTCTGGCAGATCTGAACAGTGTTACTGATATTGCTT ATGCTTCTGGCAGATCTGAACAGTGTT ATGCTTCTGGCAGAT |||||||||||||||||||| TACGAAGACCGTCTAGACTTGTCACAATGACTATAACGAA 3’
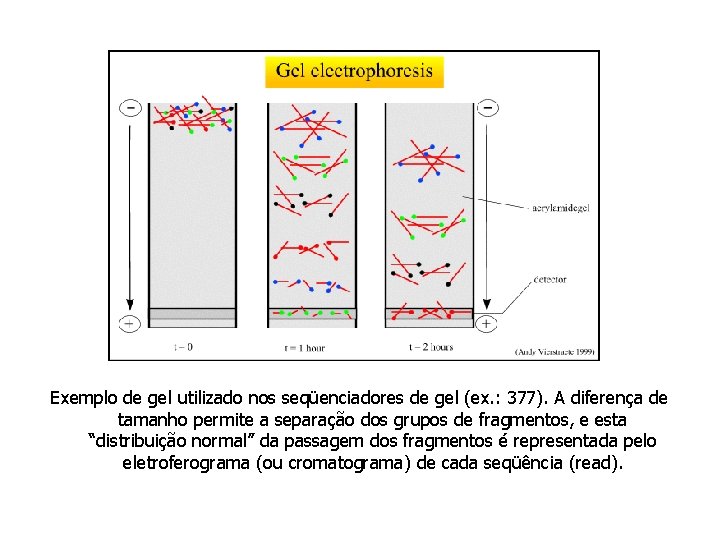
Exemplo de gel utilizado nos seqüenciadores de gel (ex. : 377). A diferença de tamanho permite a separação dos grupos de fragmentos, e esta “distribuição normal” da passagem dos fragmentos é representada pelo eletroferograma (ou cromatograma) de cada seqüência (read).
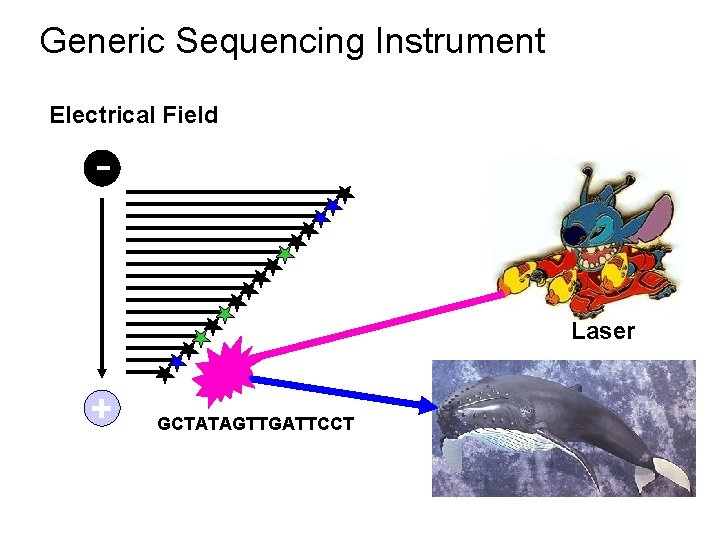
Generic Sequencing Instrument Electrical Field - Laser + GCTATAGTTGATTCCT

DYEnamic ET Terminators – Pré Mix Energy Transfer Dyes • Fluorescein Donor Dye • Standard Rhodamine Acceptor Dyes Fluorescein-R 110 -dd. GTP Fluorescein-R 6 G-dd. TTP Fluorescein-TAMRA-dd. ATP Fluorescein-ROX-dd. CTP

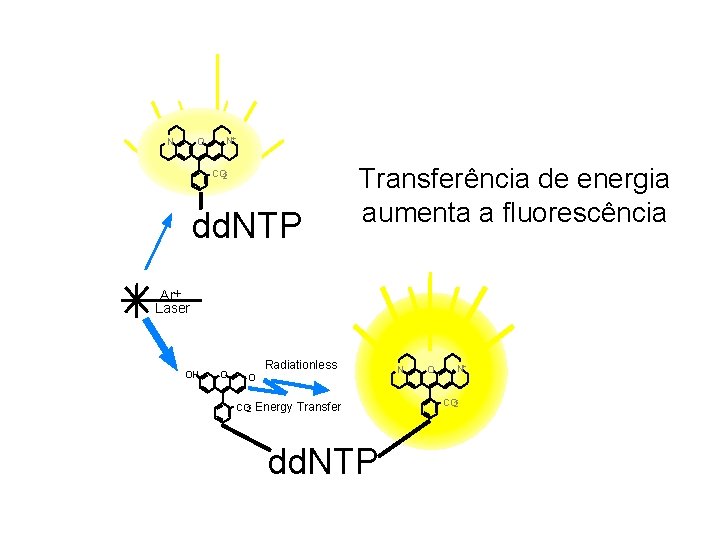
N O N+ CO 2 - dd. NTP Transferência de energia aumenta a fluorescência Ar+ Laser OH O Radiationless O CO 2 - Energy Transfer dd. NTP N O N+ CO 2 -
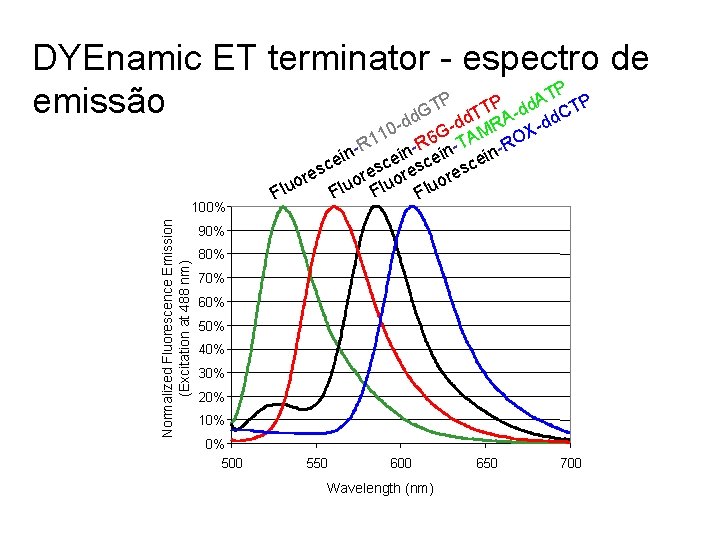
DYEnamic ET terminator - espectro de P T P A P P emissão GT d. TT A-dd d. CT d d Normalized Fluorescence Emission (Excitation at 488 nm) 100% 0 - 6 G- AMR X 1 1 R in-T n-RO R n i i in ce esce s re uor or u l luo F F 90% 80% 70% 60% 50% 40% 30% 20% 10% 0% 500 550 600 Wavelength (nm) 650 700


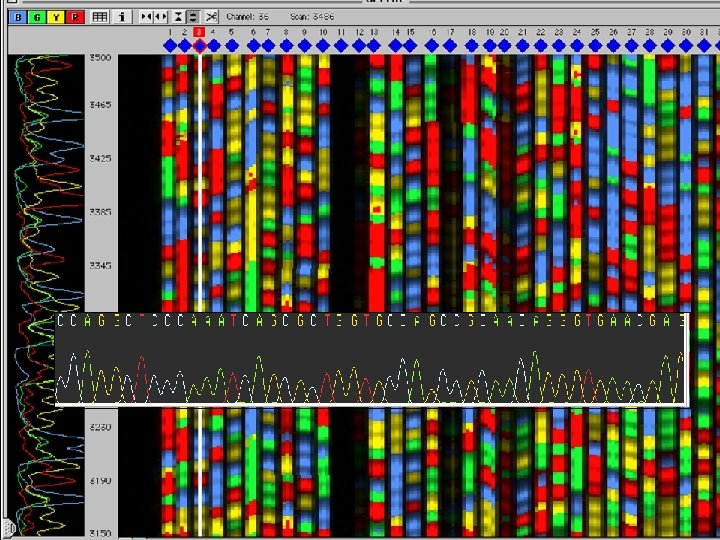

Leitura da seqüência de DNA

Análise dos resultados por Bioinformática

Montagem Limpeza das seqüências: �� remoção de seqüências ribossômicas �� remoção de seqüências de vetor �� remoção da região de poli. A �� corte por qualidade �� eliminação das derrapagens
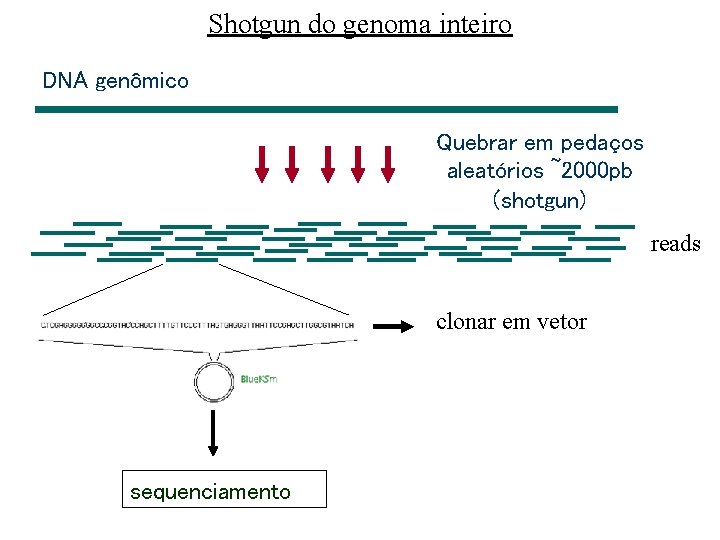
Shotgun do genoma inteiro DNA genômico Quebrar em pedaços aleatórios ~2000 pb (shotgun) reads clonar em vetor sequenciamento

Reconstrução do DNA original a partir do fragmentos (clusterização) reads Sequência consenso (DNA original) A reconstrução é feita a partir de sobreposição dos fragmentos
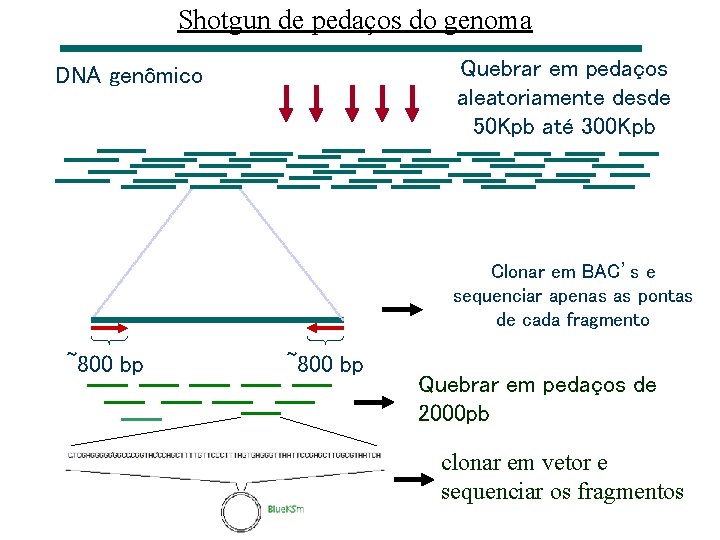
Shotgun de pedaços do genoma Quebrar em pedaços aleatoriamente desde 50 Kpb até 300 Kpb DNA genômico Clonar em BAC’s e sequenciar apenas as pontas de cada fragmento ~800 bp Quebrar em pedaços de 2000 pb clonar em vetor e sequenciar os fragmentos
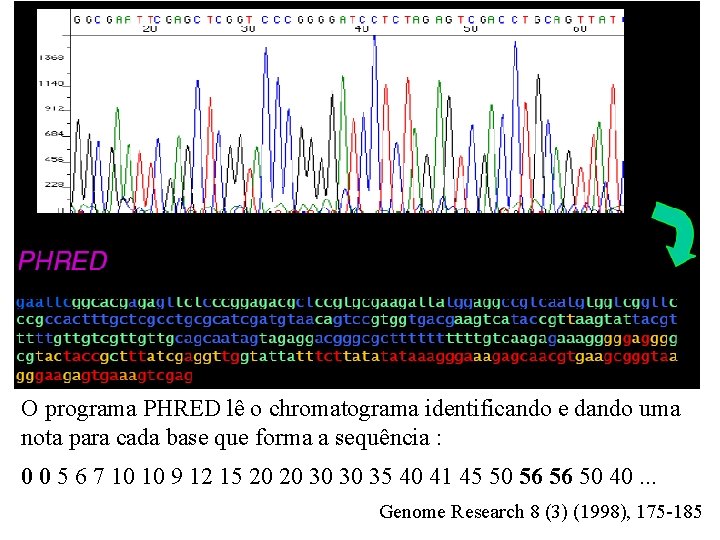
O programa PHRED lê o chromatograma identificando e dando uma nota para cada base que forma a sequência : 0 0 5 6 7 10 10 9 12 15 20 20 30 30 35 40 41 45 50 56 56 50 40. . . Genome Research 8 (3) (1998), 175 -185
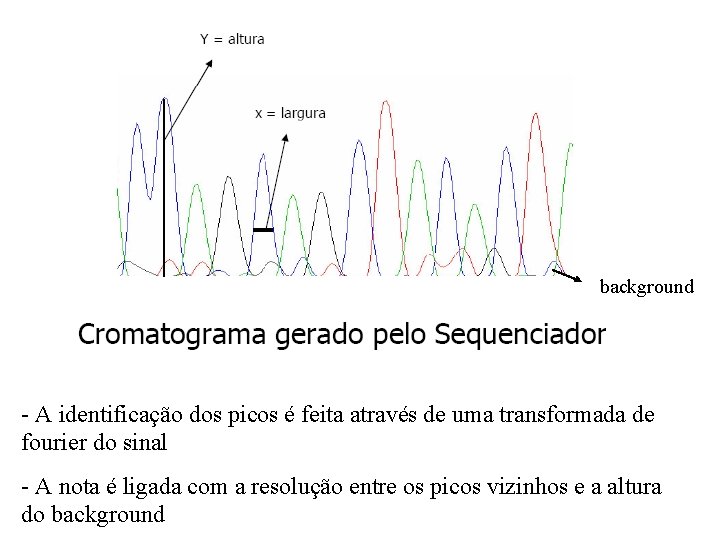
background - A identificação dos picos é feita através de uma transformada de fourier do sinal - A nota é ligada com a resolução entre os picos vizinhos e a altura do background
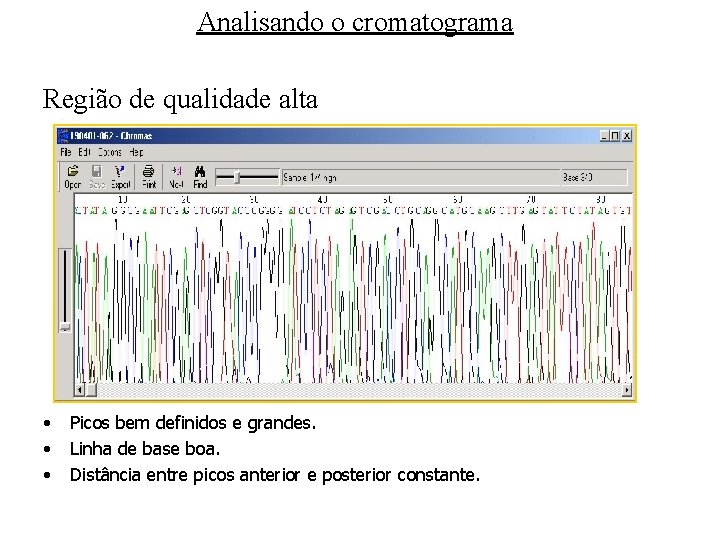
Analisando o cromatograma Região de qualidade alta • • • Picos bem definidos e grandes. Linha de base boa. Distância entre picos anterior e posterior constante.

Região de qualidade média – poucas ambigüidades • • • Picos razoavelmente bem definidos e de tamanho médio. Linha de base boa a razoável. Distância entre picos anterior e posterior razoável.

Região de qualidade baixa – baixa confiabilidade • • • Picos mal definidos e de tamanho pequeno. Linha de base confusa. Distância entre picos anterior e posterior inconstante.
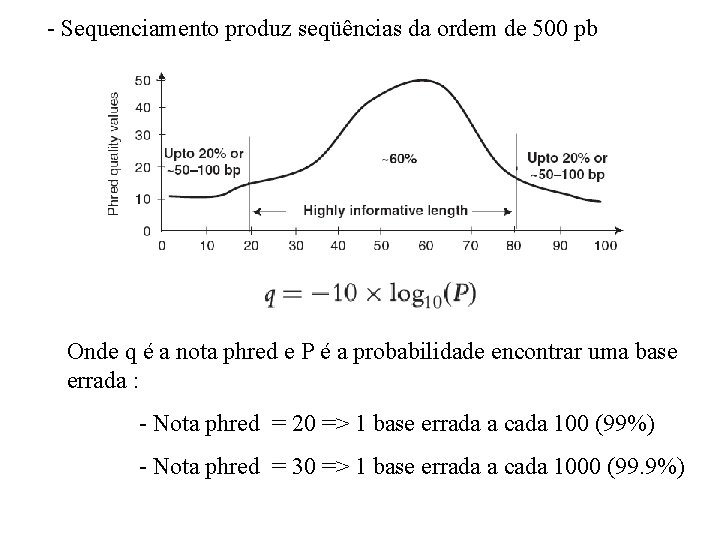
- Sequenciamento produz seqüências da ordem de 500 pb Onde q é a nota phred e P é a probabilidade encontrar uma base errada : - Nota phred = 20 => 1 base errada a cada 100 (99%) - Nota phred = 30 => 1 base errada a cada 1000 (99. 9%)

Pirosequenciamento Science 281 (1998), n. 5375, 363 -365
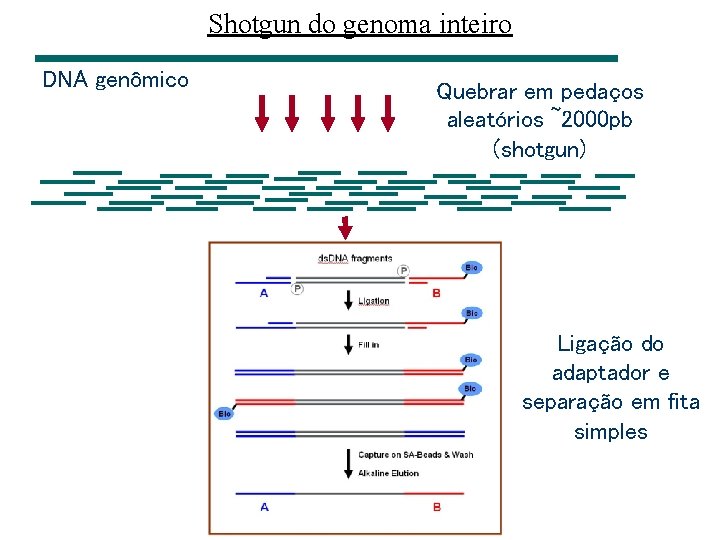
Shotgun do genoma inteiro DNA genômico Quebrar em pedaços aleatórios ~2000 pb (shotgun) Ligação do adaptador e separação em fita simples

Pirosequenciamento - O adaptador permite que o DNA se ligue em grânulos minúsculos (diâmetro de 28 mm). Apenas um DNA é ligado em cada grânulo - Os grânulos são envolvidos em gotas de óleo que contêm todos os reagentes necessários para amplificar o DNA - Cada gota contendo o grânulo é mantida isolada para evitar contaminação e consegue produzir 10 milhões de cópias numa reação de pirosequenciamento - Um pmol de DNA numa reação de pirosequenciamento produz 1011 moléculas de ATP gerando mais de 109 fótons, num comprimento de onda de 560 nm, e num período de 3 -4 segundos. Facilmente detectado por uma câmera de CCD Nature 437 (2005), 326 -327
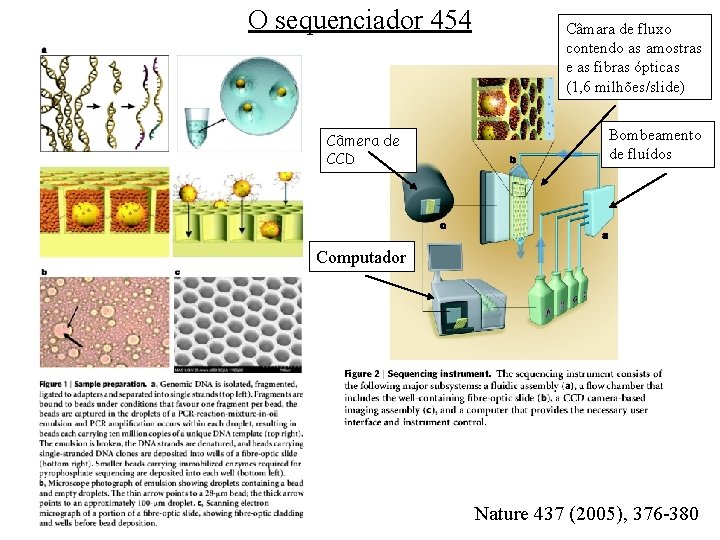
O sequenciador 454 Câmera de CCD Câmara de fluxo contendo as amostras e as fibras ópticas (1, 6 milhões/slide) Bombeamento de fluídos Computador Nature 437 (2005), 376 -380
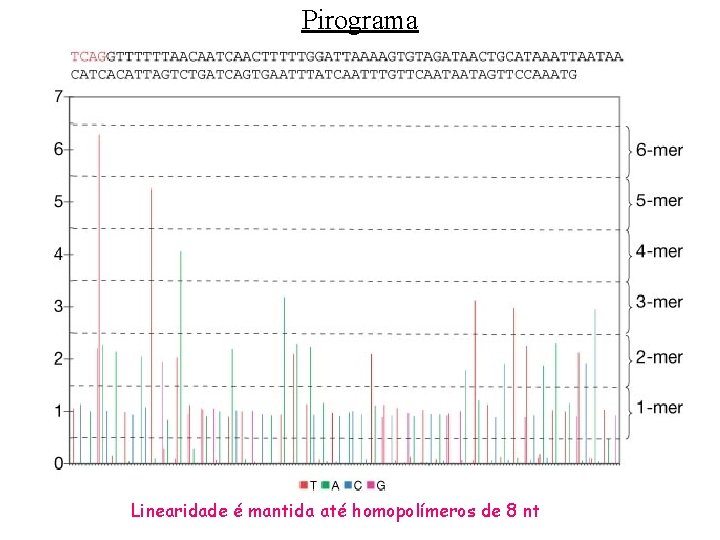
Pirograma Linearidade é mantida até homopolímeros de 8 nt
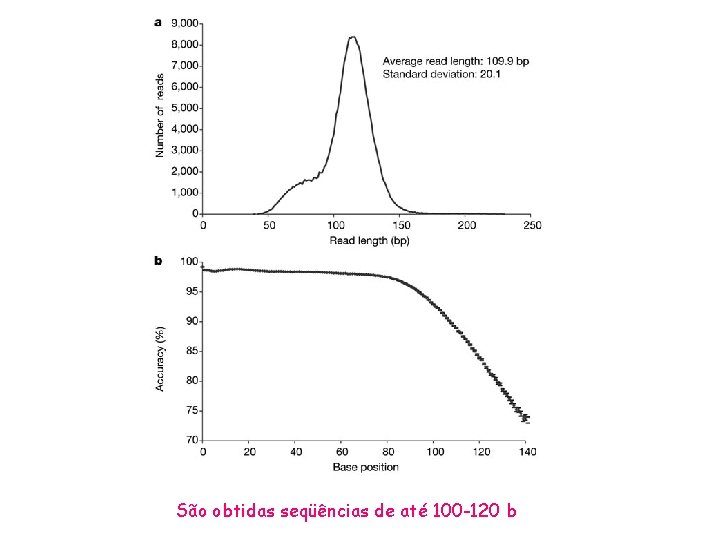
São obtidas seqüências de até 100 -120 b

Sanger vs Pirosequenciamento SANGER • Depende de clonagem em bactéria (2 semanas de trabalho) Pirosequenciamento • Não há clonagem • 1 milhão de pb em 24 horas • 25 milhões de bp em 4 horas (100 x mais rápido) • Reads de ~700 bp • Reads de ~100 bp • Clones de fita dupla permitem seqüenciamento em ambas direções (facilita orientação e montagem) • Fragmentos fita simples não permitem seqüenciamento em ambas direções • 6 meses de sequenciamento, 24 horas por dia, para sequenciar o genoma de um fungo • 24 horas para sequenciar o genoma de um fungo Conclusão : a união faz a força PNAS 103 (2006), 11240

Os organismos possuem padrões

As moléculas também.

Evolução Daehhhh! Caracteres morfológicos Macadores moleculares Sequências Similaridade X Homologia A homologia deve ser uma conclusão feita pela observação da similaridade. Transferência horizontal Um alto índice de similaridade entre as sequências justifica a conclusão de que elas são homólogas ?

1859: Charles Darwin A Origem das Espécies 1831 -1836: Viagem do Beagle

2004 -2006: Viagem do Sorcerer II

Animações • http: //www. dnalc. org/ddnalc/resources/sangers eq. html • http: //www. dnalc. org/ddnalc/resources/cycseq. html
- Slides: 54