SELEO NATURAL A NVEL MOLECULAR Dilvan Moreira Baseado

SELEÇÃO NATURAL A NÍVEL MOLECULAR Dilvan Moreira (Baseado em material do prof. André Carvalho)

Leitura Introduction to Computational Genomics: A Case Studies Approach Capítulo 6

Conteúdo 3 Motivação Evolução e Seleção Natural HIV x Sistema Imune Humano Quantificando a seleção natural Regiões sinônimas e não-sinônimas Estudo de caso André de Carvalho - ICMC/USP 15/06/2021

AIDS 4 Reportada pela primeira vez nos Estados Unidos em 1979 Reconhecida como uma doença transmissível em 1981 Denominada Acquired Immune Deficiency Syndrome (AIDS) HIV (Human immunodeficiency Virus) foi reconhecido em 1983 como agente infeccioso 20 milhões de pessoas mortas até hoje André de Carvalho - ICMC/USP 15/06/2021
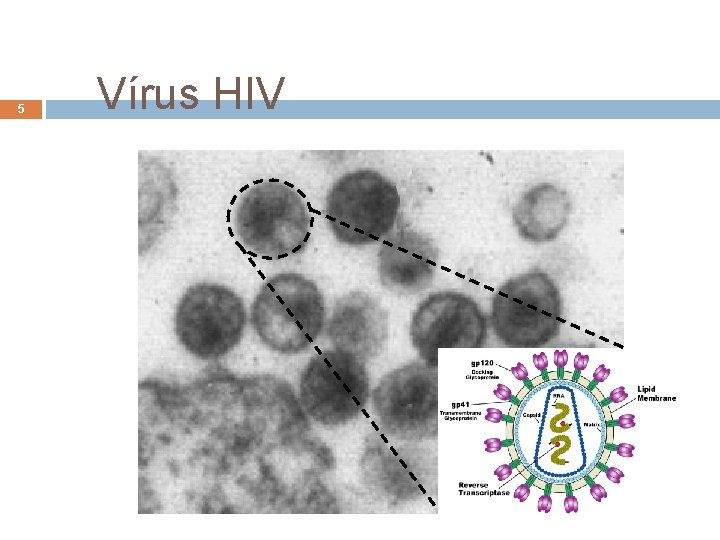
5 Vírus HIV André de Carvalho - ICMC/USP 15/06/2021
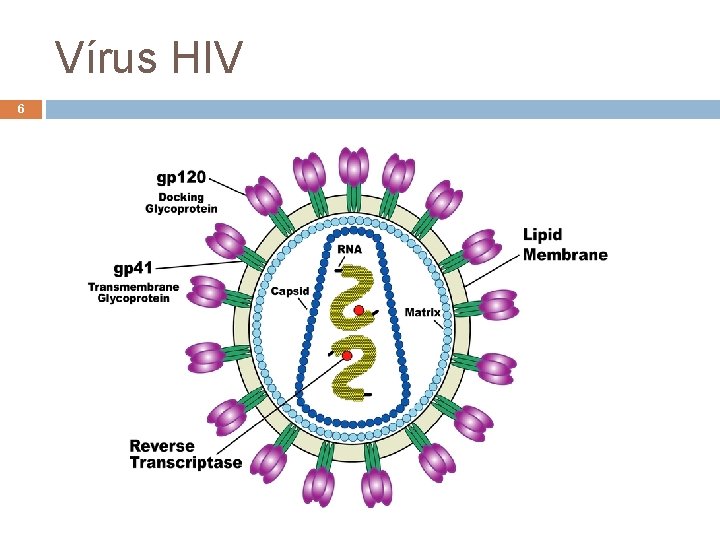
Vírus HIV 6 André de Carvalho - ICMC/USP 15/06/2021

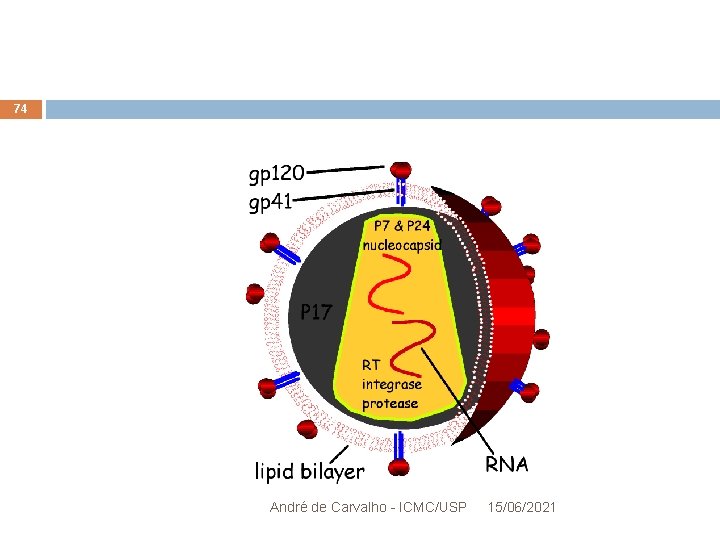
Vírus HIV 7 Retrovírus Vírus envelopado com genoma de RNA que se replica por intermédio do DNA Possui a enzima transcriptase reversa Faz a transcrição reversa de seu genoma para DNA é depois integrado com o genoma do hospedeiro por uma enzima integrase André de Carvalho - ICMC/USP 15/06/2021
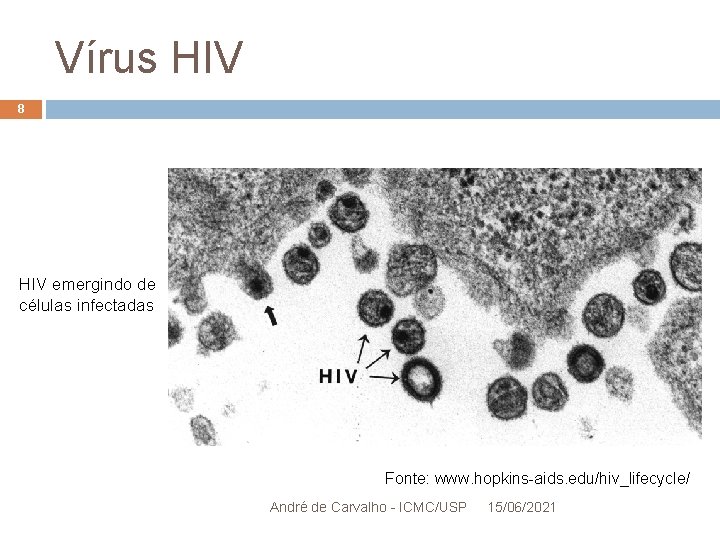
Vírus HIV 8 HIV emergindo de células infectadas Fonte: www. hopkins-aids. edu/hiv_lifecycle/ André de Carvalho - ICMC/USP 15/06/2021
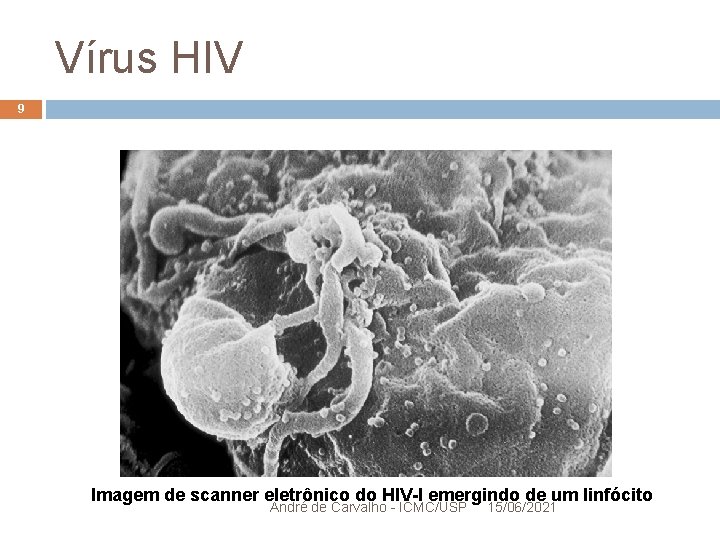
Vírus HIV 9 Imagem de scanner eletrônico do HIV-I emergindo de um linfócito André de Carvalho - ICMC/USP 15/06/2021
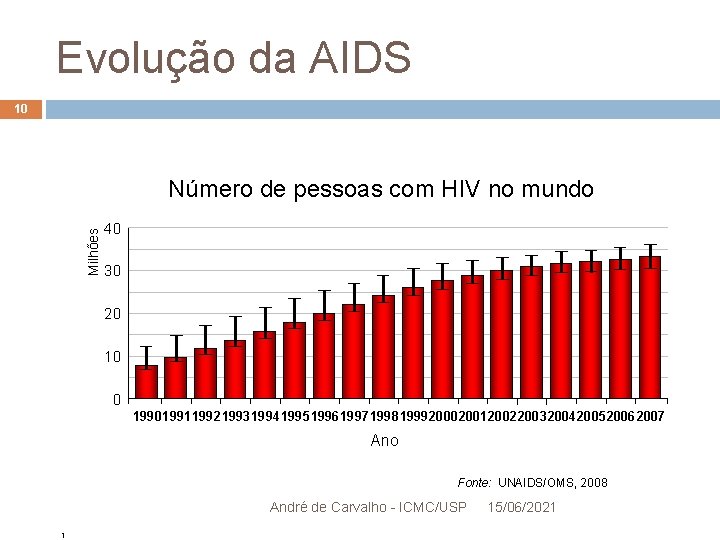
Evolução da AIDS 10 Milhões Número de pessoas com HIV no mundo 40 30 20 10 0 1991 1992 1993 1994 1995 1996 1997 1998 1999 2000 2001 2002 2003 2004 2005 2006 2007 Ano Fonte: UNAIDS/OMS, 2008 André de Carvalho - ICMC/USP 1 15/06/2021
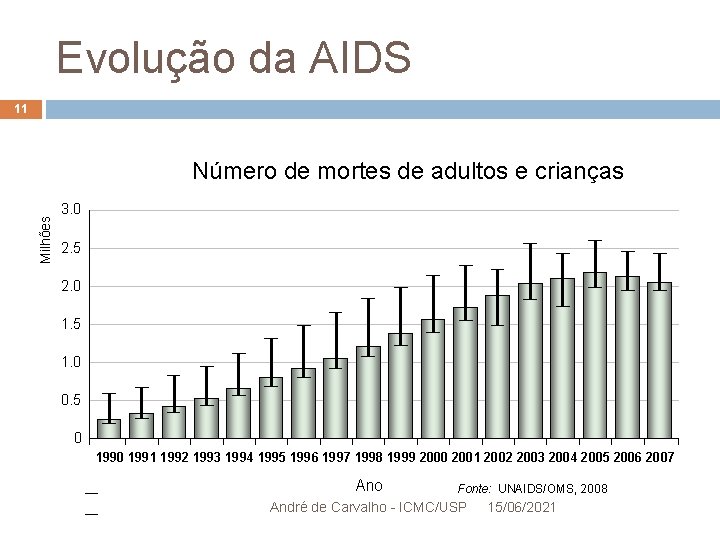
Evolução da AIDS 11 Milhões Número de mortes de adultos e crianças 3. 0 2. 5 2. 0 1. 5 1. 0 0. 5 0 1991 1992 1993 1994 1995 1996 1997 1998 1999 2000 2001 2002 2003 2004 2005 2006 2007 Ano Fonte: UNAIDS/OMS, 2008 André de Carvalho - ICMC/USP 15/06/2021
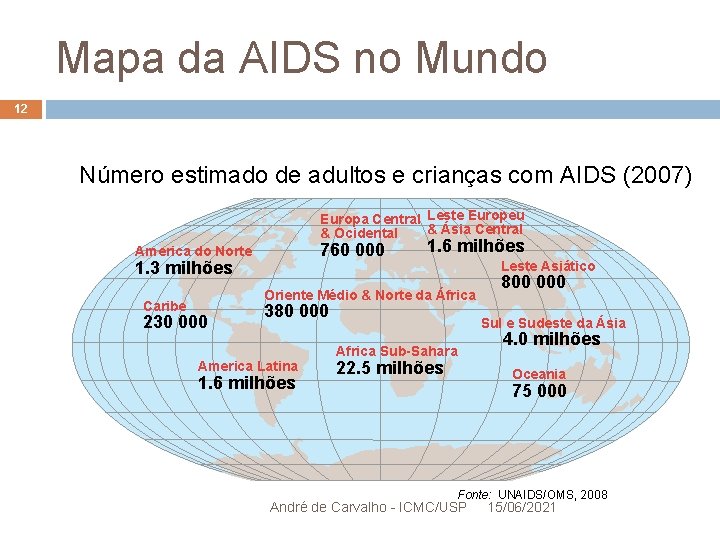
Mapa da AIDS no Mundo 12 Número estimado de adultos e crianças com AIDS (2007) Europa Central Leste Europeu & Ásia Central & Ocidental 760 000 America do Norte 1. 3 milhões Caribe 1. 6 milhões Leste Asiático Oriente Médio & Norte da África 230 000 380 000 America Latina 1. 6 milhões 800 000 Sul e Sudeste da Ásia Africa Sub-Sahara 22. 5 milhões 4. 0 milhões Oceania 75 000 Fonte: UNAIDS/OMS, 2008 André de Carvalho - ICMC/USP 15/06/2021
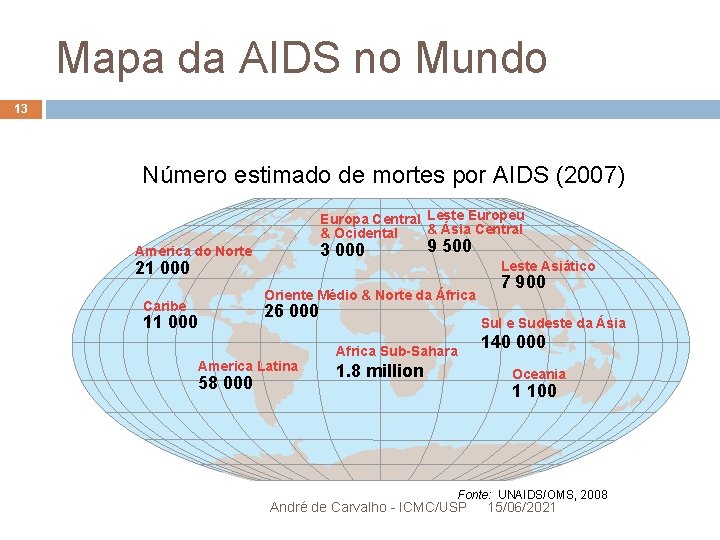
Mapa da AIDS no Mundo 13 Número estimado de mortes por AIDS (2007) Europa Central Leste Europeu & Ásia Central & Ocidental 3 000 America do Norte 21 000 9 500 Leste Asiático Oriente Médio & Norte da África Caribe 11 000 26 000 America Latina 58 000 7 900 Sul e Sudeste da Ásia Africa Sub-Sahara 1. 8 million 140 000 Oceania 1 100 Fonte: UNAIDS/OMS, 2008 André de Carvalho - ICMC/USP 15/06/2021

AIDS 14 Não há cura nem vacina efetiva Existem medicamentos para manter o vírus sob controle São caros Mecanismos para destruir um vírus: Sistema imune Medicamentos Como o HIV consegue escapar das tentativas de destruí-lo? André de Carvalho - ICMC/USP 15/06/2021

AIDS 15 Evoluindo (modificando seu genoma) em um período muito curto de tempo que mata o paciente vírus que o infectou Vírus tem: Taxas de mutação muito altas Tempo de duplicação (geração) muito curto André de Carvalho - ICMC/USP 15/06/2021

Evolução e Seleção Natural 16 Evolução de uma seqüência de DNA: Por meio de mutações Que passam para as próximas gerações Seleção natural ajuda a retardar ou acelerar a taxa de evolução André de Carvalho - ICMC/USP 15/06/2021

Evolução e Seleção Natural 17 Vários outros vírus e bactérias apresentam resistência a medicamentos e ao sistema imune Seleção natural adaptativa Charles Darwin, 1859: On the origin of species by means of natural selection André de Carvalho - ICMC/USP 15/06/2021

Evolução e Seleção Natural 18 Seleção natural no nível de organismos: Indivíduos melhor adaptados para sobreviver e reproduzir geram mais descendentes para a próxima geração Seleção natural no nível molecular: Remove mutações nocivas Seleção negativa ou purificadora Favorece a propagação de mutações vantajosas Seleção positiva André de Carvalho - ICMC/USP 15/06/2021

Evolução e Seleção Natural 19 Para a evolução ocorrer é preciso: Que os indivíduos da população tenham características geneticamente controladas bastante variadas Que essas características afetem a capacidade de sobrevivência ou reprodução dos indivíduos André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 20 HIV: Envoltório de proteína com duas cópias do genoma Fita de RNA com 9. 5 Kb e apenas 9 genes Retrovírus: RNA -> DNA -> vírus Reconhece e infecta linfócitos T André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 21 Sistema imune humano: Quando há infecção, encontra e mata as células infectadas Linfócitos T identificam as células infectadas “Aprendem” a identificar e marcar cada inimigo André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 22 HIV ataca justamente as células que deveriam identificá-lo para ser destruído Como funciona: Células infectadas ficam marcadas com trechos de proteína do vírus (epitopes) Que ficam visíveis na membrana da célula Se os linfócitos T reconhecem um epitope específico, a célula pode ser destruída Senão, o vírus se reproduz André de Carvalho - ICMC/USP 15/06/2021
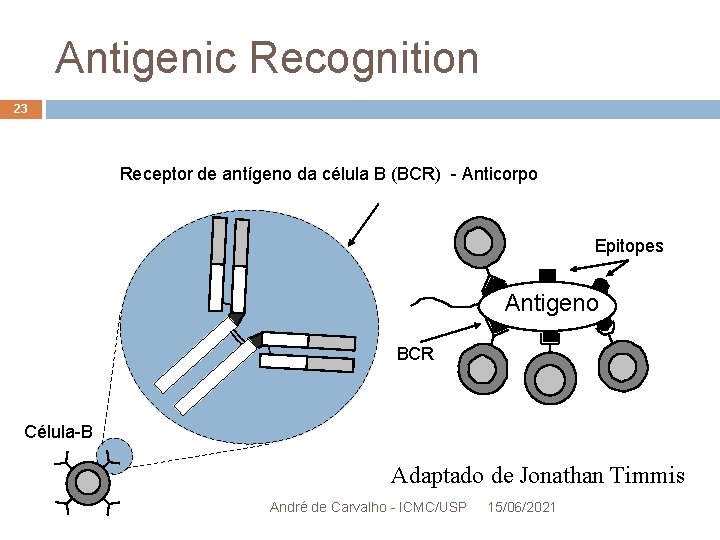
Antigenic Recognition 23 Receptor de antígeno da célula B (BCR) - Anticorpo Epitopes Antigeno BCR Célula-B Adaptado de Jonathan Timmis André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 24 Como funciona? HIV gera novos indivíduos com novas versões dos epitopes: Os vírus com epitopes que o tornam “invisível” sobrevivem Mutações muito vantajosas Sistema imune “vai aprendendo” a identificar novos epitopes Demora alguns dias André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 25 Como funciona? HIV se reproduz extremamente rápido: 1, 5 dias Replicação no vírus é muito propensa a erros: Taxa de erro: 5 mutações a cada 100. 000 pb a cada geração 1000 vezes maior que nos humanos Resultado: muita variação genética em poucas gerações e em pouco tempo André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 26 Como funciona? Velocidade com que o sistema imune consegue reconhecer novos epitopes < Velocidade com que o HIV evolui gerando indivíduos “invisíveis” Resultado: Não há imunidade permanente (como acontece com outros vírus e bactérias) André de Carvalho - ICMC/USP 15/06/2021

HIV x Sistema Imune Humano 27 Seleção natural positiva agiu quando: Epitopes reconhecidas reduzem a aptidão (fitness) de um indivíduo Mutações que tornam o vírus invisível aumentam essa aptidão Vírus com essas mutações sobrevivem e geram mais descendentes para as próximas gerações André de Carvalho - ICMC/USP 15/06/2021

28 Quantificando a Seleção Natural Mutações que surgem em um indivíduo podem se tornar fixas na população A maioria das mutações fixas são neutras A maioria das mutações não neutras interferem na função das proteínas Mudam aminoácidos Prejudiciais ao funcionamento do organismo 80 -90% dessas mutações são danosas Muito poucas mutações são vantajosas Mas são importantes para a evolução André de Carvalho - ICMC/USP 15/06/2021

29 Quantificando a Seleção Natural Como saber quais mutações são neutras, nocivas ou vantajosas? Medir a aptidão de indivíduos com novas mutações em laboratório Só é possível com organismos de vida muito curta e com grandes populações Alternativa: Comparar a taxa de substituição das mutações que podem mudar uma proteína com a taxa em áreas que não afetam as proteínas André de Carvalho - ICMC/USP 15/06/2021

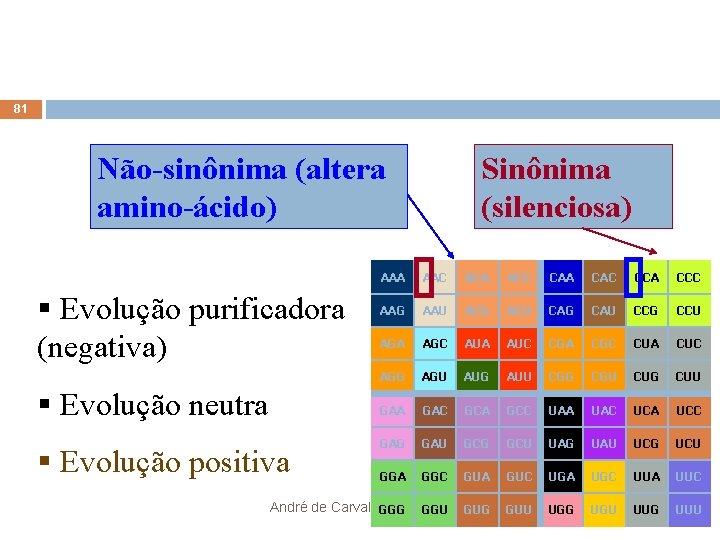
30 Quantificando a Seleção Natural Forma mais comum é comparar: Mutações sinônimas: Alteram a seqüência do códon, mas não mudam o aminoácido na tradução GTT (Val) → GTA (Val) Mutações não sinônimas: Alteram o aminoácido após a tradução GTT (Val) → GCT (Ala) André de Carvalho - ICMC/USP 15/06/2021

31 Quantificando a Seleção Natural 2 a base no códon C A G G Mutações na primeira posição raramente são sinônimas (5%) C A Phe Leu Leu Leu Ile Ile Met Val Val Ser Ser Pro Pro Thr Thr Ala Ala Tyr Cys T Tyr Cys C Parada A Mutações na segunda Parada Trp G His Arg T posição nunca são His Arg C sinônimas Gln Arg A Gln Arg G Mutações na terceira Asn Ser T posição são, na Asn Ser C maioria das vezes, Lys Arg A sinônimas Lys Arg G Asp Gly T Asp Gly C Glu André de Gly Carvalho -AICMC/USP 15/06/2021 Glu Gly G 3 a base no códon 1 a base no códon T T

32 Quantificando a Seleção Natural Não-sinônima (altera AA) § Evolução purificadora (negativa) § Evolução neutra § Evolução positiva Sinônima (silenciosa) AAA AAC ACA ACC CAA CAC CCA CCC AAG AAU ACG ACU CAG CAU CCG CCU AGA AGC AUA AUC CGA CGC CUA CUC AGG AGU AUG AUU CGG CGU CUG CUU GAA GAC GCA GCC UAA UAC UCA UCC GAG GAU GCG GCU UAG UAU UCG UCU GGA GGC GUA GUC UGA UGC UUA UUC GGG GGU GUG GUU UGG UGU UUG UUU André de Carvalho - ICMC/USP 15/06/2021

33 Quantificando a Seleção Natural Taxas de substituições sinônimas e não sinônimas são proporcionais a taxa de mutação A diferença entre elas se deve à diferentes taxas de aceitação Conseqüência da seleção natural Como há mais substituições não sinônimas nas regiões codificadoras, usa-se: KA: # subs. não sinônimas/sítios não sinônimos KS: # subs. sinônimas/sítios sinônimos André de Carvalho - ICMC/USP 15/06/2021

34 Quantificando a Seleção Natural Motoo Kimura (1977): Raciocínio: Comparação entre as substituições não-sinônimas em um gene (KA/KS) mostra a força e a forma da seleção natural Mutações vantajosas são muito raras Mutações nocivas não se propagam na população Portanto: maioria das mutações são neutras Quanto mais forte for a seleção negativa, menos substituições não-sinônimas serão observadas André de Carvalho - ICMC/USP 15/06/2021

35 Quantificando a Seleção Natural Neutras? Como? Sejam: f 0: Em um período de tempo t: fração das mutações não-sinônimas neutras v: taxa de mutação KA = v f 0 t KS = v t (todas as mutações sinônimas são neutras) KA / K S = f 0 Quanto maior a seleção negativa, menor f 0 Assim, KA / KS < 1 (geralmente entre 0 e 0. 3) André de Carvalho - ICMC/USP 15/06/2021

36 Quantificando a Seleção Natural Se KA / KS = 1 f 0=1 Se considerar mutações não-sinônimas vantajosas: Ex: Proteina sem utilidade KA / KS pode ser maior que 1 Seja a proporção de mutações vantajosas KA = v (f 0 + )t KA / K S = f 0 + Combinação das substituições neutras e vantajosas André de Carvalho - ICMC/USP 15/06/2021

37 Quantificando a Seleção Natural Assim, KA / KS dá uma medida da ação da seleção natural nos genes: KA / KS < 1: predomina a seleção negativa KA / KS > 1: predomina a seleção positiva KA / KS = 1: as seleções negativa e positiva se cancelam Obs: as taxas podem ter comportamento diferente em diferentes trechos dos genes André de Carvalho - ICMC/USP 15/06/2021

Como Estimar KA/KS? 38 Alternativas: Métodos de aproximação rápidos Abordagens estatísticas mais complexas Baseadas na máxima verossimilhança Bias Transições e transversões Uso de códon e nucleotídeo André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 39 Métodos de estimação mais simples: Conta número de sítios sinônimos e não-sinônimos nas duas seqüências (Sc e Ac) Conta número de diferenças sinônimas e nãosinônimas entre as duas seqüências (Sd e Ad) Calcula os números de substituições por posição Aplica correção de Jukes e Cantor para múltiplas substituições Obtém KA/KS André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 40 Sítios sinônimos e não-sinônimos: Idéia artificial Sítios sinônimos têm a propensão a apresentar mutações sinônimas Sítios não-sinônimos têm a propensão a apresentar mutações não-sinônimas André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 41 Algoritmo Nei-Gojobori (1986) Um dos mais simples Assume: Taxas de transversões e transições iguais Que o uso dos códons não é tendencioso Entrada: duas seqüências homólogas Saída: KA e KS André de Carvalho - ICMC/USP 15/06/2021

Algoritmo Nei-Gojobori 42 Alinhar as duas seqüências Usando somente os códons sem gaps 1: calcular Ac e Sc (números de sítios A e S) 2: calcular Ad e Sd (números de diferenças A e S) 3: calcular KA e KS Custo: linear no comprimento das seqüências André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 43 Passo 1: calculando Ac e Sc (sítios) ck: k-ésimo códon sc (ck): número de sítios sinônimos no códon ck ac (ck): número de sítios não-sinônimos no códon ck f i: fração de mudanças de i-ésima posição de um códon que resulta em uma mudança sinônima (i = 1, 2, 3) André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 44 Exemplo: códon TTA (leucina) i T T A 1 2 3 Para i = 1 T -> A gera ATA (Ile): não-sinônima T -> C gera CTA (Leu): sinônima T -> G gera GTA (Val): não-sinônima f 1 = 1/3 André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 45 Exemplo: códon TTA (leucina) i T T A 1 2 3 Para i = 2 T -> A gera TAA (parada): não-sinônima T -> C gera TCA (Ser): não-sinônima T -> G gera TGA (parada): não-sinônima f 2 = 0/3 André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 46 Exemplo: códon TTA (leucina) i T T A 1 2 3 Para i = 3 A -> T gera TTT (Phe): não-sinônima A -> C gera TTC (Phe): não-sinônima A -> G gera TTG (Leu): sinônima f 3 = 1/3 André de Carvalho - ICMC/USP 15/06/2021
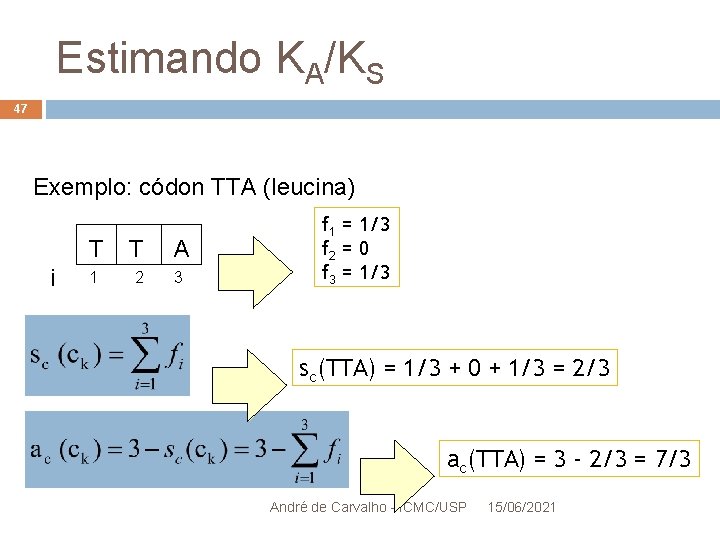
Estimando KA/KS 47 Exemplo: códon TTA (leucina) i T T A 1 2 3 f 1 = 1/3 f 2 = 0 f 3 = 1/3 sc(TTA) = 1/3 + 0 + 1/3 = 2/3 ac(TTA) = 3 - 2/3 = 7/3 André de Carvalho - ICMC/USP 15/06/2021
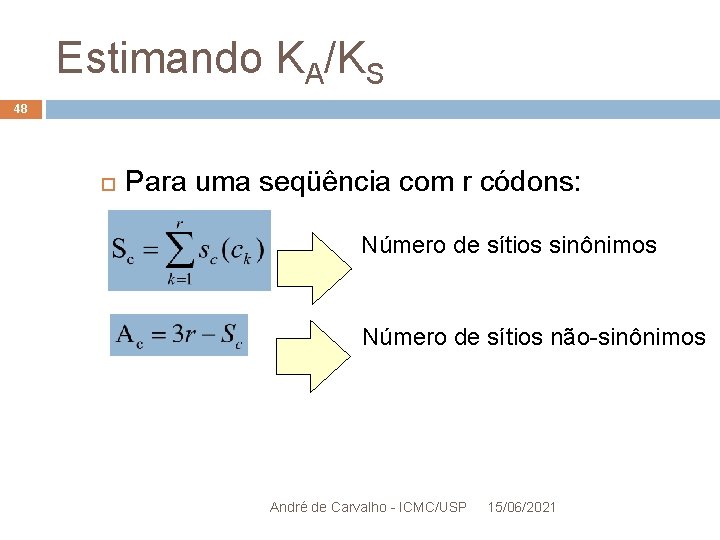
Estimando KA/KS 48 Para uma seqüência com r códons: Número de sítios sinônimos Número de sítios não-sinônimos André de Carvalho - ICMC/USP 15/06/2021
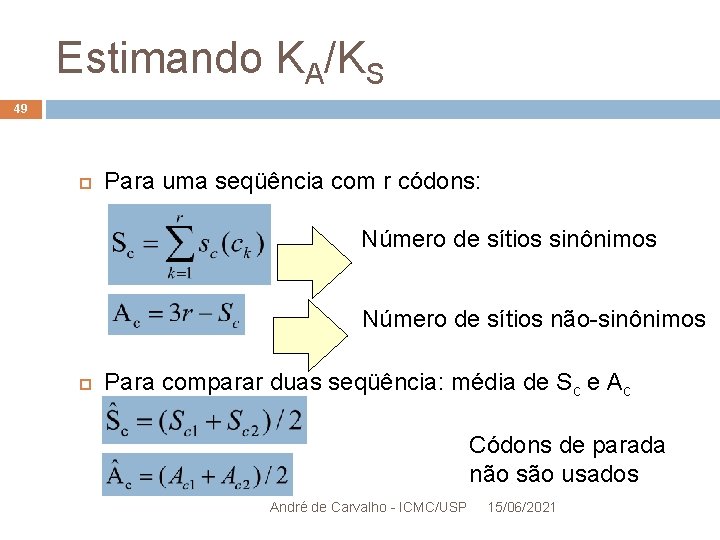
Estimando KA/KS 49 Para uma seqüência com r códons: Número de sítios sinônimos Número de sítios não-sinônimos Para comparar duas seqüência: média de Sc e Ac Códons de parada não são usados André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 50 Passo 2: calculando Ad e Sd (diferenças) sd (ck): número de diferenças sinônimas no códon ck ad (ck): número de diferenças não-sinônimas no códon ck A diferença entre as duas seqüências em um códon pode ser de 1, 2 ou 3 nucleotídeos André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 51 Diferença de 1 nucleotídeo: Decisão imediata se substituição é sinônima ou nãosinônima Ex. : G T T - (Val) G T A - (Val) 1 diferença Mesmo aminoácido Substituição sinônima sd(ck) = 1 ad (ck) = 0 André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 52 Diferença de 2 nucleotídeos: Há 2 caminhos para obter as diferenças observadas Imaginar 2 caminhos de evolução levando do primeiro para o segundo códon Assumir probabilidade igual para os caminhos Calcular sd (ck) e ad (ck) para cada caminho Calcular a média dos dois caminhos André de Carvalho - ICMC/USP 15/06/2021

Exemplo 53 T T T - (Phe) G T A - (Val) André de Carvalho - ICMC/USP 15/06/2021

Exemplo 54 2 caminhos possíveis : T T T - (Phe) G T A - (Val) 2 diferenças André de Carvalho - ICMC/USP 15/06/2021
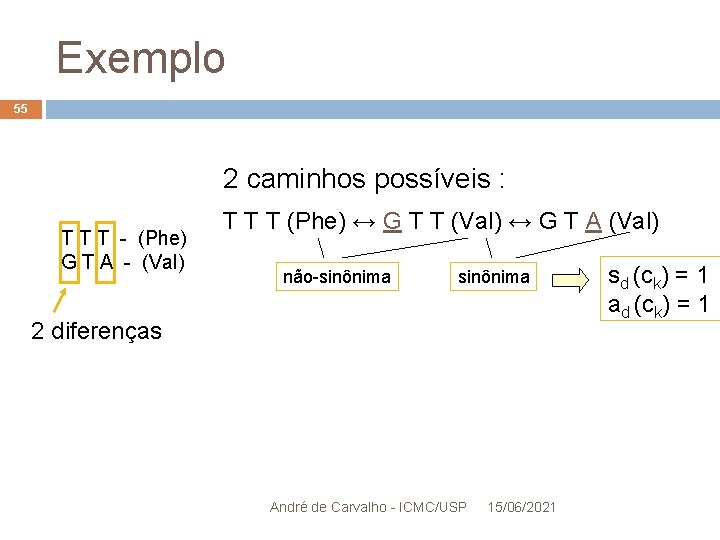
Exemplo 55 2 caminhos possíveis : T T T - (Phe) G T A - (Val) T T T (Phe) ↔ G T T (Val) ↔ G T A (Val) não-sinônima 2 diferenças André de Carvalho - ICMC/USP 15/06/2021 sd (ck) = 1 ad (ck) = 1
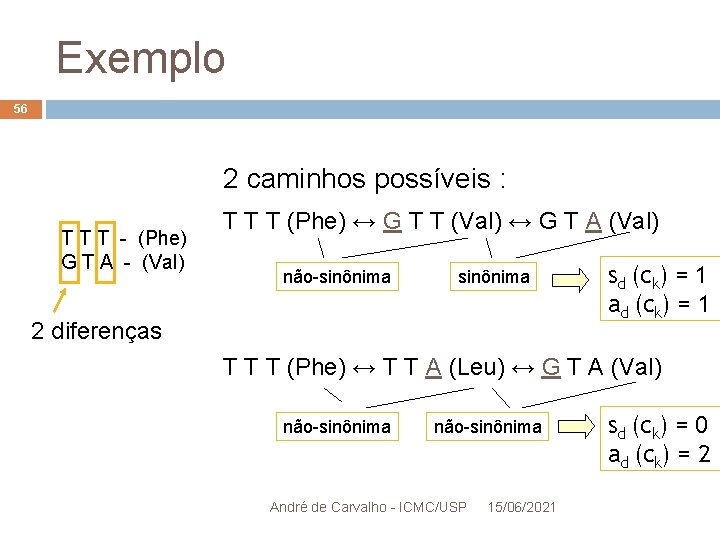
Exemplo 56 2 caminhos possíveis : T T T - (Phe) G T A - (Val) T T T (Phe) ↔ G T T (Val) ↔ G T A (Val) não-sinônima 2 diferenças sd (ck) = 1 ad (ck) = 1 T T T (Phe) ↔ T T A (Leu) ↔ G T A (Val) não-sinônima André de Carvalho - ICMC/USP 15/06/2021 sd (ck) = 0 ad (ck) = 2
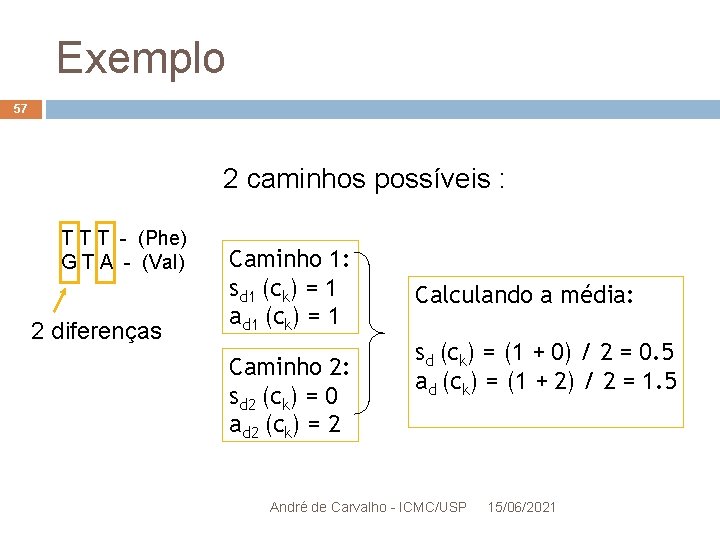
Exemplo 57 2 caminhos possíveis : T T T - (Phe) G T A - (Val) 2 diferenças Caminho 1: sd 1 (ck) = 1 ad 1 (ck) = 1 Caminho 2: sd 2 (ck) = 0 ad 2 (ck) = 2 Calculando a média: sd (ck) = (1 + 0) / 2 = 0. 5 ad (ck) = (1 + 2) / 2 = 1. 5 André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 58 Diferença de 3 nucleotídeos: Há 6 caminhos possíveis, com três passos cada Calcula sd (ck) e ad (ck) para cada caminho Calcula a média de sd (ck) e ad (ck) nos 6 caminhos André de Carvalho - ICMC/USP 15/06/2021
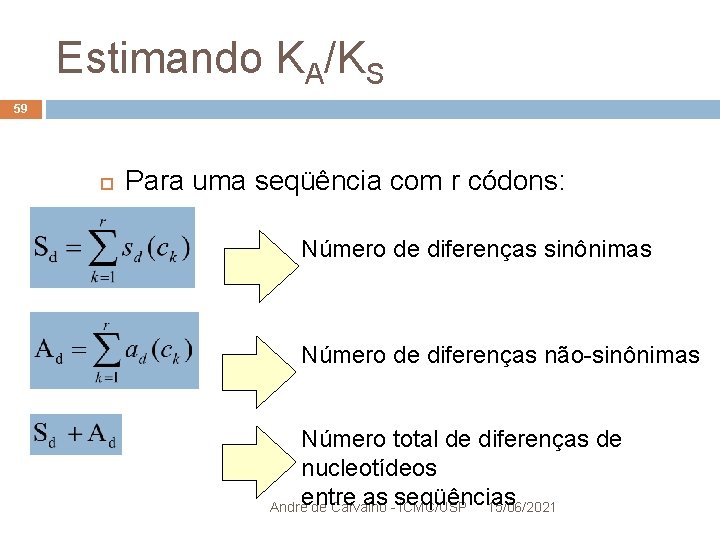
Estimando KA/KS 59 Para uma seqüência com r códons: Número de diferenças sinônimas Número de diferenças não-sinônimas Número total de diferenças de nucleotídeos entre as seqüências André de Carvalho - ICMC/USP 15/06/2021

Estimando KA/KS 60 Passo 3: calculando KA e KS ds: proporção de diferenças sinônimas da: proporção de diferenças não-sinônimas Aplicando a correção de Jukes e Cantor a ds e da, obtem-se, respectivamente, KA e KS André de Carvalho - ICMC/USP 15/06/2021

Estudo de Caso: Seleção Natural e HIV 61 Genoma de centenas de indivíduos sequenciados Muitas mudanças em regiões reconhecidas pelo sistema imune Para escapar das células de defesa Seleção positiva Regiões invariáveis, para manter as funções biológicas do vírus Seleção negativa André de Carvalho - ICMC/USP 15/06/2021

Estudo de Caso: Seleção Natural e HIV 62 Analisar KA/KS em vários genes e regiões diferentes de um mesmo gene Ajuda a entender que regiões do genoma do HIV estão sofrendo evolução adaptativa André de Carvalho - ICMC/USP 15/06/2021
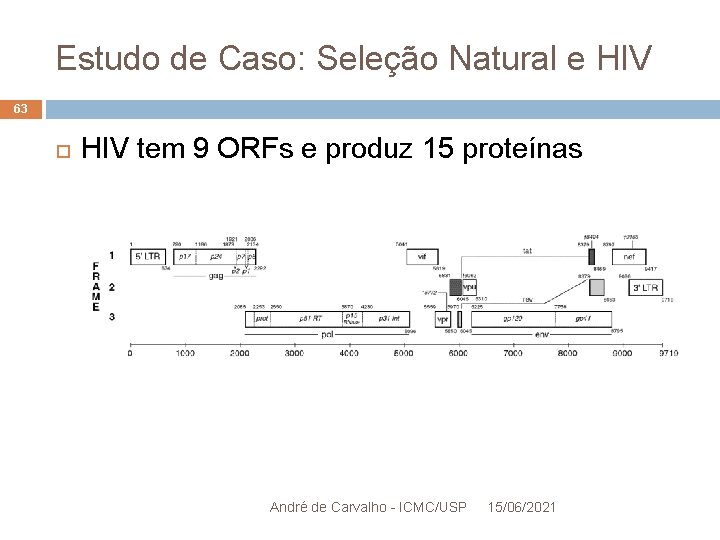
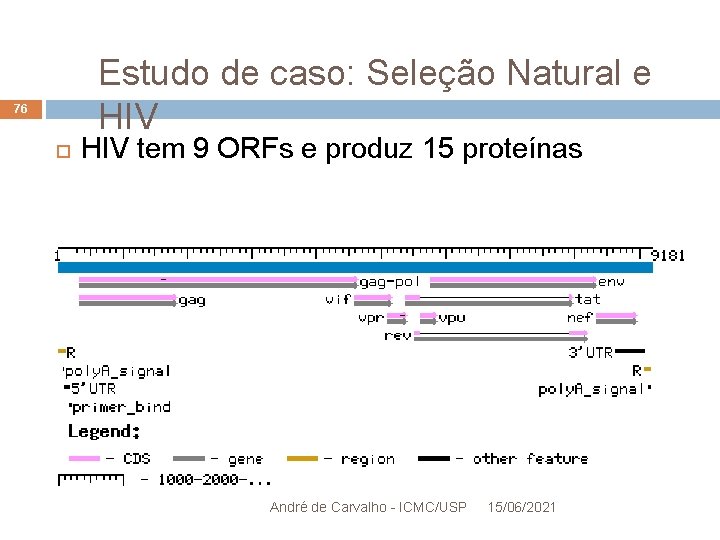
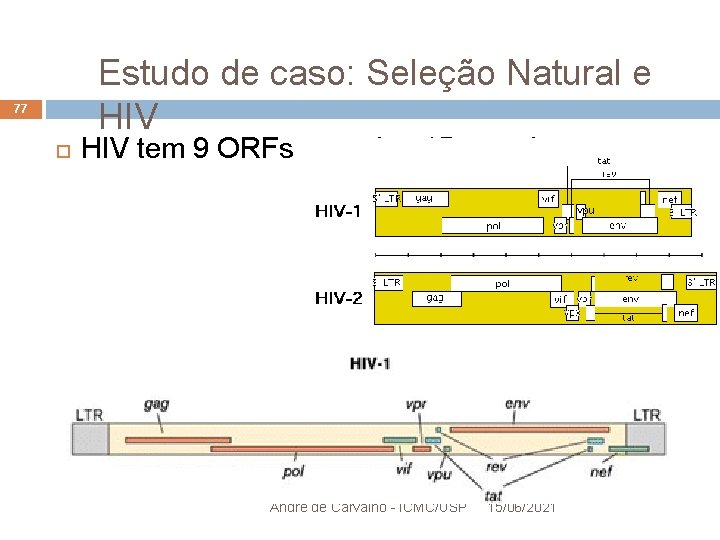
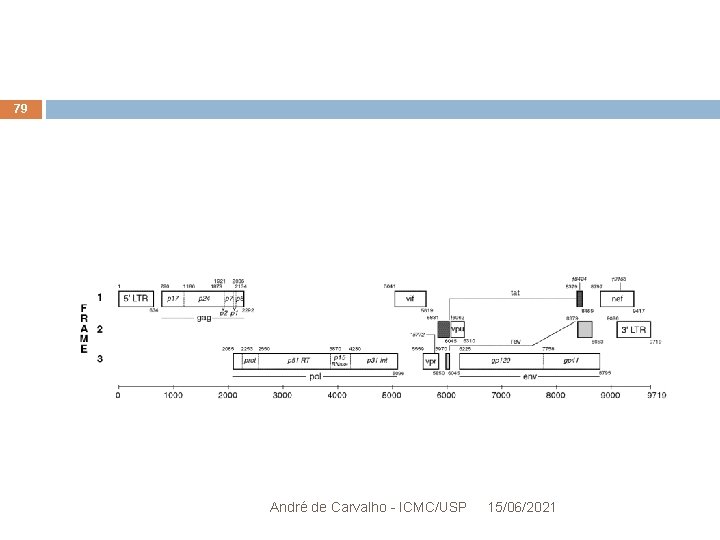
Estudo de Caso: Seleção Natural e HIV 63 HIV tem 9 ORFs e produz 15 proteínas André de Carvalho - ICMC/USP 15/06/2021

Estudo de Caso: Seleção Natural e HIV 64 Análise: 1º passo: encontrar as ORFs 2º passo: calcular KA/KS Usar 2 seqüências Alinhar as ORFS correspondentes, nas duas seqüências Calcular a razão para cada ORF André de Carvalho - ICMC/USP 15/06/2021

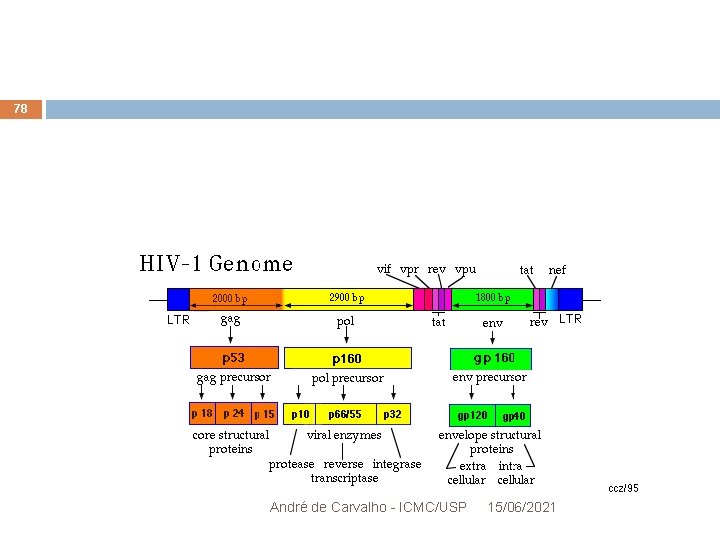
Estudo de Caso: Seleção Natural e HIV 65 Seleção natural nos epitopes: Gene ENV Codifica a glicoproteína gp 160 (envoltório do vírus) – precursora das proteínas: gp 41 gp 120: Se liga aos receptores dos linfócitos T (ajuda o vírus a reconhecer o hospedeiro) Reconhecida pelo sistema imune para indicar infecção pelo vírus André de Carvalho - ICMC/USP 15/06/2021

Estudo de Caso: Seleção Natural e HIV 66 A seleção em gp 120 precisa: Manter a capacidade de reconhecimento do hospedeiro Evitar a detecção pelo sistema imune Medir KA/KS no gene todo Oculta ambos os processos, dando um valor médio André de Carvalho - ICMC/USP 15/06/2021

Estudo de Caso: Seleção Natural e HIV 67 Para observar o que ocorre em cada parte do gene: Usar pequenas janelas para percorrer o gene e calcular KA/KS de cada trecho Deslizando a janela em todo o gene É possível ter uma noção dos diferentes níveis de pressão seletiva em diferente partes do gene André de Carvalho - ICMC/USP 15/06/2021
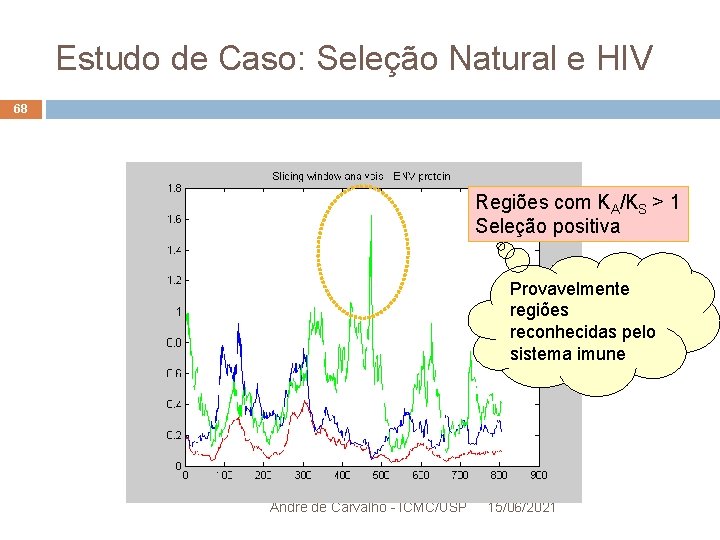
Estudo de Caso: Seleção Natural e HIV 68 Regiões com KA/KS > 1 Seleção positiva Provavelmente regiões reconhecidas pelo sistema imune André de Carvalho - ICMC/USP 15/06/2021

Estudo de Caso: Seleção Natural e HIV 69 Visualização da evolução rápida do HIV usando árvore filogenética André de Carvalho - ICMC/USP 15/06/2021

Conclusão 70 AIDS e HIV Evolução e Seleção Natural HIV x Sistema Imune Humano Quantificando a seleção natural Regiões sinônimas e não-sinônimas Estudo de caso André de Carvalho - ICMC/USP 15/06/2021
Perguntas?

72 André de Carvalho - ICMC/USP 15/06/2021
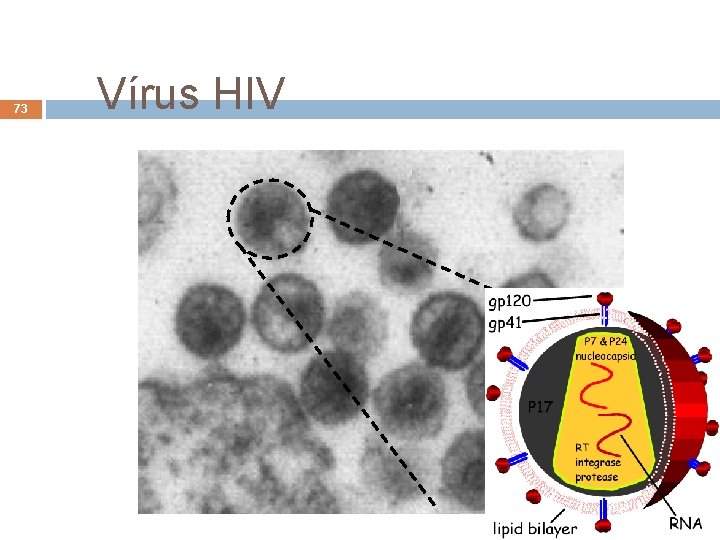
73 Vírus HIV André de Carvalho - ICMC/USP 15/06/2021
74 André de Carvalho - ICMC/USP 15/06/2021

Ciclo de Replicação do HIV 75 André de Carvalho - ICMC/USP 15/06/2021
Estudo de caso: Seleção Natural e HIV 76 HIV tem 9 ORFs e produz 15 proteínas André de Carvalho - ICMC/USP 15/06/2021
Estudo de caso: Seleção Natural e HIV 77 HIV tem 9 ORFs e produz 15 proteínas André de Carvalho - ICMC/USP 15/06/2021
78 André de Carvalho - ICMC/USP 15/06/2021
79 André de Carvalho - ICMC/USP 15/06/2021

Codon Models 80 Combine information from both DNA and protein levels Synonymous (silent ) Non-synonymous (amino-acid altering) AAA AAC ACA ACC CAA CAC CCA CCC AAG AAU ACG ACU CAG CAU CCG CCU AGA AGC AUA AUC CGA CGC CUA CUC AGG AGU AUG AUU CGG CGU CUG CUU GAA GAC GCA GCC UAA UAC UCA UCC GAG GAU GCG GCU UAG UAU UCG UCU GGA GGC GUA GUC UGA UGC UUA UUC André de Carvalho - ICMC/USP GGG GGU GUG 15/06/2021 GUU UGG UGU UUG UUU § Purifying evolution § Neutral evolution § Positive Darwinian evolution
81 Não-sinônima (altera amino-ácido) Sinônima (silenciosa) AAA AAC ACA ACC CAA CAC CCA CCC AAG AAU ACG ACU CAG CAU CCG CCU AGA AGC AUA AUC CGA CGC CUA CUC AGG AGU AUG AUU CGG CGU CUG CUU GAA GAC GCA GCC UAA UAC UCA UCC GAG GAU GCG GCU UAG UAU UCG UCU GGA GGC GUA GUC UGA UGC UUA UUC André de Carvalho - ICMC/USP GGG GGU GUG 15/06/2021 GUU UGG UGU UUG UUU § Evolução purificadora (negativa) § Evolução neutra § Evolução positiva

82 Estudo de caso: Seleção Natural e HIV André de Carvalho - ICMC/USP 15/06/2021
- Slides: 82