RESAUBER Gestion Durable des rsistances gntiques Ralstonia solanacearum

RESAUBER: « Gestion Durable des résistances génétiques à Ralstonia solanacearum chez l’aubergine » Réunion finale 24 mai 2017

Action 1: Typologie des situations épidémiologiques Tâche 1. 1. Production et fourniture de matériel végétal (sources de résistance) INRA-GAFL Tâche 1. 2. Phénotypage multilocal des sources de résistance TECHNISEM, ARMEFLHOR, CIRAD-Guyane

Tâche 1. 1: Production et fourniture de matériel végétal (sources de résistance) par l’INRA-GAFL (MC Daunay) • Semences Core-TEP Ø semences produites et envoyées aux partenaires RESAUBER pour tests résistance (Réunion, Cameroun, Guyane) • Générations F 1, F 2 et BC et témoins Ø semences envoyés au CIRAD Réunion et à Technisem-Cameroun pour tests résistance sur générations et pour témoins essais carto génétique • Lignées RILs (E 8 x E 6) Ø semences envoyées au CIRAD et à Technisem-Cameroun pour essais carto génétique • Lignées HD (E 4 x E 8) et HD (E 3 x E 8) Ø semences envoyées au CIRAD et à Technisem-Cameroun pour essais carto génétique

Tâche 1. 2: Phénotypage multilocal des sources de résistance TECHNISEM au Cameroun (Morgane Raynal) Ø 1 essai avec 3 répétitions réalisé en 2014 -2015 En infestation naturelle renforcée (phylotype III-29) CIRAD à La Guyane (Jean Guyot & Fabien Doare) Ø 1 essai avec 3 répétitions finalisé au 2ème semestre 2016 en infestation artificielle (phylotype IIB-4 NPB) ARMEFLHOR à La Réunion (Thomas Deslandes) Ø 1 essai avec 3 répétitions réalisé en 2016 en infestation naturelle (phylotype I)
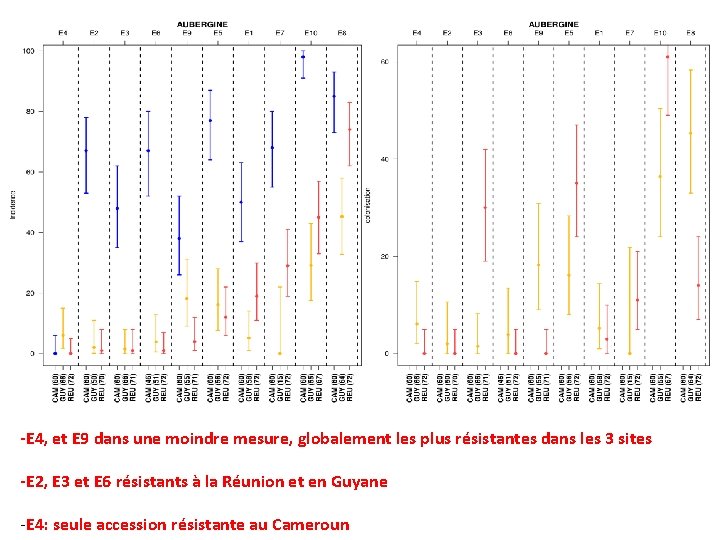
-E 4, et E 9 dans une moindre mesure, globalement les plus résistantes dans les 3 sites -E 2, E 3 et E 6 résistants à la Réunion et en Guyane -E 4: seule accession résistante au Cameroun
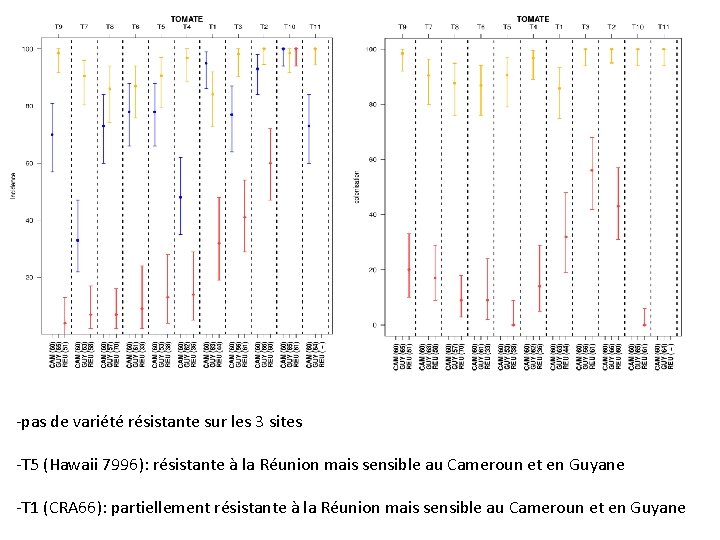
-pas de variété résistante sur les 3 sites -T 5 (Hawaii 7996): résistante à la Réunion mais sensible au Cameroun et en Guyane -T 1 (CRA 66): partiellement résistante à la Réunion mais sensible au Cameroun et en Guyane
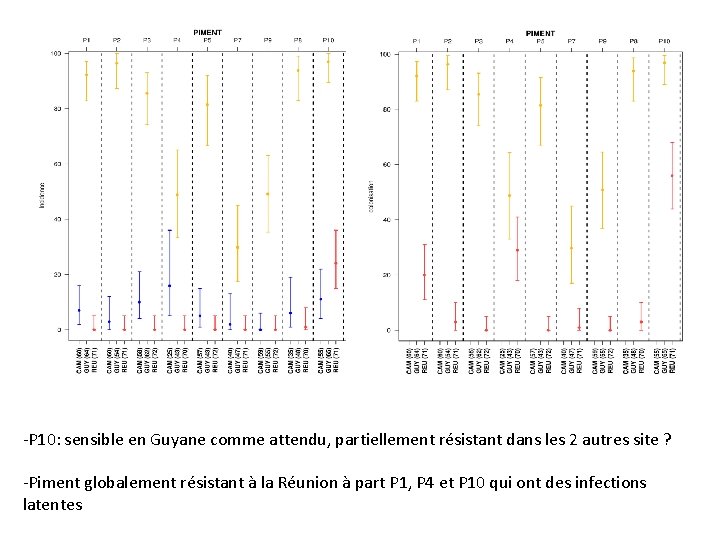
-P 10: sensible en Guyane comme attendu, partiellement résistant dans les 2 autres site ? -Piment globalement résistant à la Réunion à part P 1, P 4 et P 10 qui ont des infections latentes

BILAN de l’ACTION 1 Les sources de résistance de la core. TEP ont été caractérisées dans les 3 sites partenaires outremer Fortes variations entre sites observées sur les 3 espèces Globalement mêmes tendances observées que celles observées en chambre climatique par Lebeau et al (2011) La caractérisation moléculaire des populations pathogènes a été réalisée à la Réunion, au Cameroun mais pas en Guyane Accessions d’aubergine les plus résistantes: -Réunion: E 2, E 3, E 4, E 6, E 9 -Cameroun: E 4 -Guyane: E 2, E 3, E 4, E 6

Action 2: Spécificité de la résistance d’AG 91 -25 (E 6) et recherche de facteurs de résistance complémentaires Tâche 2. 1: Dissection génétique de la résistance à RS dans une population de lignées RILs issue du croisement (E 8 x. E 6) vs. la diversité génétique de la bactérie CIRAD-Réunion, TECHNISEM Tâche 2. 2: Etude de sources de résistance alternatives vs. souches virulentes de Phylotypes I contournant ERs 1 CIRAD Réunion, TECHNISEM Tâche 2. 3: Production de descendances de lignées fixées par haplo-diploïdisation en vue de recher des QTL de résistance à ces souches virulentes INRA-GAFL Ces différentes tâches ont fait l’objet de la thèse de Doctorat de Sylvia SALGON (Avril 2014 -mai 2017) assurée par un financement CIFRE, CASDARCIRAD-ARMEFLHOR et du stage élève-ingénieur d’Edith GAROT
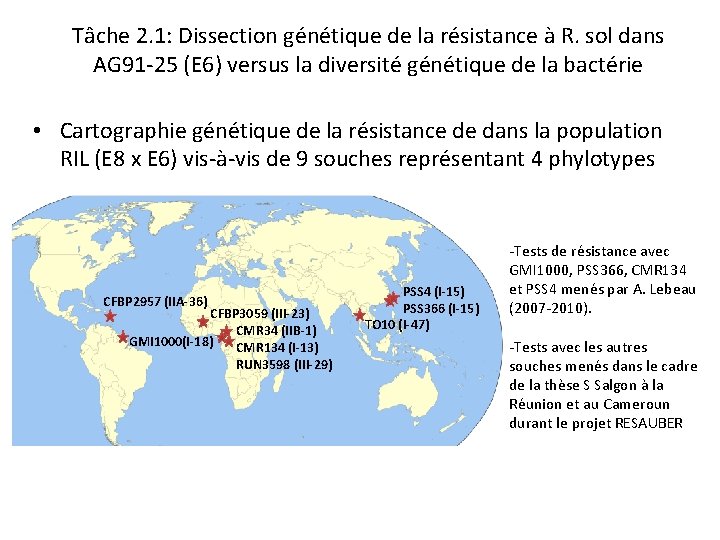
Tâche 2. 1: Dissection génétique de la résistance à R. sol dans AG 91 -25 (E 6) versus la diversité génétique de la bactérie • Cartographie génétique de la résistance de dans la population RIL (E 8 x E 6) vis-à-vis de 9 souches représentant 4 phylotypes CFBP 2957 (IIA-36) CFBP 3059 (III-23) CMR 34 (IIB-1) GMI 1000(I-18) CMR 134 (I-13) RUN 3598 (III-29) PSS 4 (I-15) PSS 366 (I-15) TO 10 (I-47) -Tests de résistance avec GMI 1000, PSS 366, CMR 134 et PSS 4 menés par A. Lebeau (2007 -2010). -Tests avec les autres souches menés dans le cadre de la thèse S Salgon à la Réunion et au Cameroun durant le projet RESAUBER

Tâche 2. 1: Dissection génétique de la résistance à RS dans une population de lignées RILs issue du croisement (E 8 x. E 6) vs. la diversité génétique de la bactérie • Cartographie fine de la résistance de E 6 vis-à-vis des 8 souches Ø Détection des QTLs: Chr 09 ü ERs 1: Positionné sur le chr 09 dans une zone de 0, 57 c. M ü Marqueurs ancres flanquant ERs 1 avec position physique connue sur les génomes de tomate et aubergine ü Position physique estimée dans un intervalle de 1, 7 Mbp ü ERs 1 détecté spécifiquement vs 3 souches du phylotype 1

Tâche 2. 1: Dissection génétique de la résistance à RS dans une population de lignées RILs issue du croisement (E 8 x. E 6) vs. la diversité génétique de la bactérie • Cartographie fine de la résistance de E 6 vis-à-vis de 8 souches Ø Détection des QTLs: Chr 05_b Ø 1 QTL à effet majeur sur le chr. 5 détecté vs 2 souches virulentes : CFBP 3059 (III) and CFBP 2957 (IIA) Ø 1 QTL généraliste détecté sur le chr. 2 vs 4 souches virulentes : PSS 4 and TO 10 (I), CFBP 3059 (III) et CFBP 2957 (IIA) Chr 02

Tâche 2. 2: Etude de sources de résistance alternatives vs. les souches virulentes de phylotypes I contournant ERs 1 • Phénotypage de la population HD (E 4 x E 8) réalisé à La Réunion Ø 2 essais ont été réalisés vs PSS 4 (I-15)(thèse de Sylvia Salgon) • Phénotypage de la population HD (E 3 x E 8) réalisé à La Réunion Ø 2 essais ont été réalisés vs PSS 4 (I-15)(thèse S Salgon et stage d’Edith Garot) • Cartographie de la résistance de ‘Surya’ (E 4) et ‘Ceylan’ (E 3) réalisée à l’aide des cartes GBS produites en parallèle à la Réunion (thèse S Salgon)
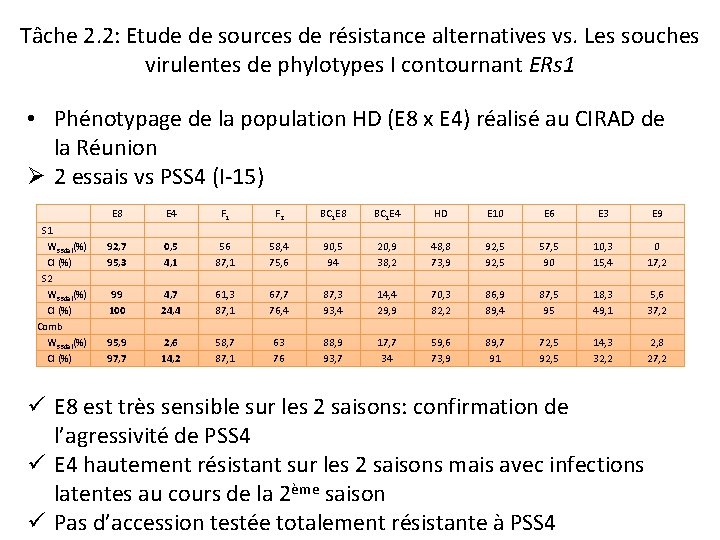
Tâche 2. 2: Etude de sources de résistance alternatives vs. Les souches virulentes de phylotypes I contournant ERs 1 • Phénotypage de la population HD (E 8 x E 4) réalisé au CIRAD de la Réunion Ø 2 essais vs PSS 4 (I-15) S 1 W 33 dai(%) CI (%) S 2 W 33 dai(%) CI (%) Comb W 33 dai(%) CI (%) E 8 E 4 F 1 F 2 BC 1 E 8 BC 1 E 4 HD E 10 E 6 E 3 E 9 92, 7 95, 3 0, 5 4, 1 56 87, 1 58, 4 75, 6 90, 5 94 20, 9 38, 2 48, 8 73, 9 92, 5 57, 5 90 10, 3 15, 4 0 17, 2 99 100 4, 7 24, 4 61, 3 87, 1 67, 7 76, 4 87, 3 93, 4 14, 4 29, 9 70, 3 82, 2 86, 9 89, 4 87, 5 95 18, 3 49, 1 5, 6 37, 2 95, 9 97, 7 2, 6 14, 2 58, 7 87, 1 63 76 88, 9 93, 7 17, 7 34 59, 6 73, 9 89, 7 91 72, 5 92, 5 14, 3 32, 2 2, 8 27, 2 ü E 8 est très sensible sur les 2 saisons: confirmation de l’agressivité de PSS 4 ü E 4 hautement résistant sur les 2 saisons mais avec infections latentes au cours de la 2ème saison ü Pas d’accession testée totalement résistante à PSS 4
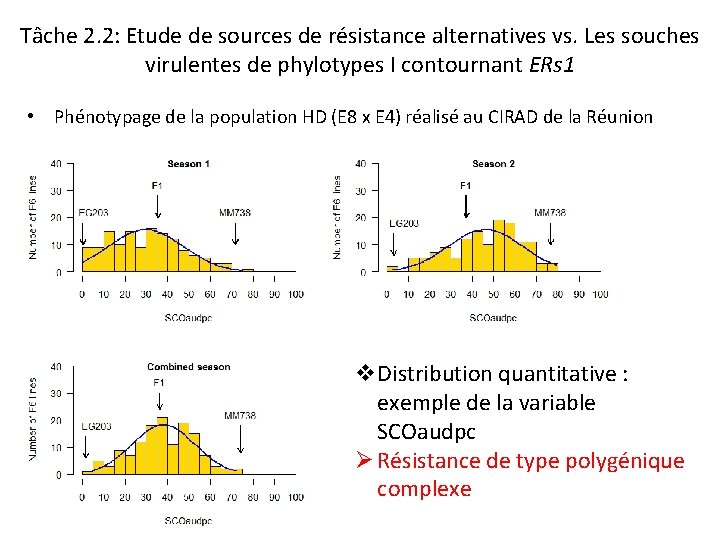
Tâche 2. 2: Etude de sources de résistance alternatives vs. Les souches virulentes de phylotypes I contournant ERs 1 • Phénotypage de la population HD (E 8 x E 4) réalisé au CIRAD de la Réunion v. Distribution quantitative : exemple de la variable SCOaudpc Ø Résistance de type polygénique complexe
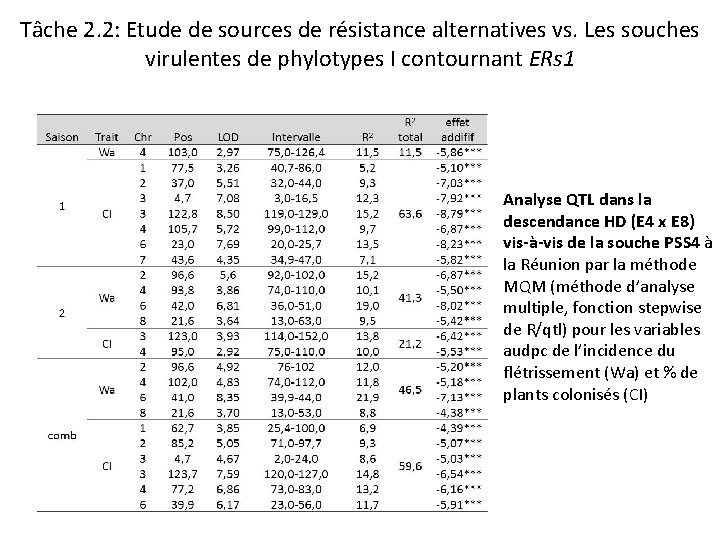
Tâche 2. 2: Etude de sources de résistance alternatives vs. Les souches virulentes de phylotypes I contournant ERs 1 Analyse QTL dans la descendance HD (E 4 x E 8) vis-à-vis de la souche PSS 4 à la Réunion par la méthode MQM (méthode d’analyse multiple, fonction stepwise de R/qtl) pour les variables audpc de l’incidence du flétrissement (Wa) et % de plants colonisés (CI)
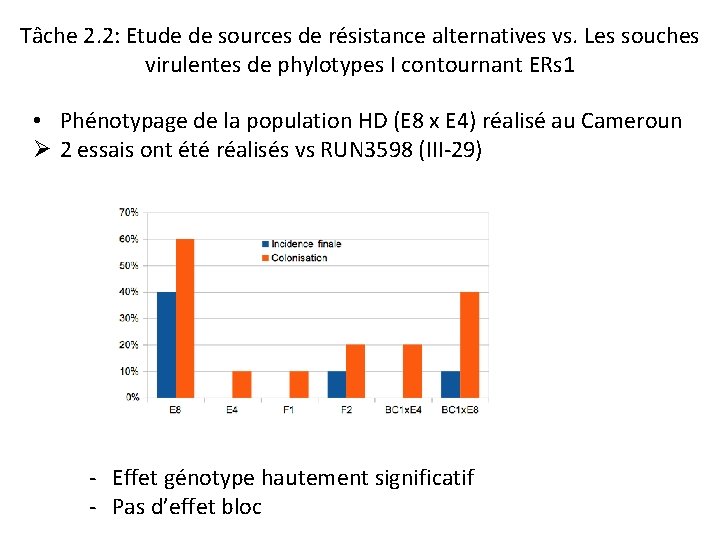
Tâche 2. 2: Etude de sources de résistance alternatives vs. Les souches virulentes de phylotypes I contournant ERs 1 • Phénotypage de la population HD (E 8 x E 4) réalisé au Cameroun Ø 2 essais ont été réalisés vs RUN 3598 (III-29) - Effet génotype hautement significatif - Pas d’effet bloc
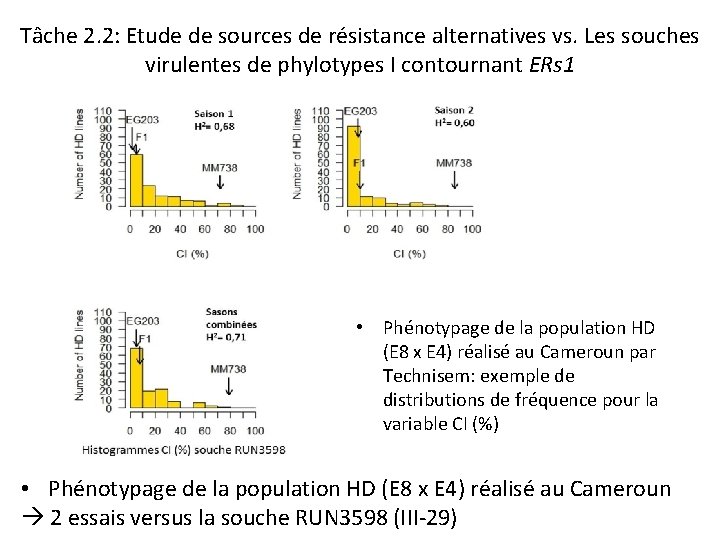
Tâche 2. 2: Etude de sources de résistance alternatives vs. Les souches virulentes de phylotypes I contournant ERs 1 • Phénotypage de la population HD (E 8 x E 4) réalisé au Cameroun par Technisem: exemple de distributions de fréquence pour la variable CI (%) • Phénotypage de la population HD (E 8 x E 4) réalisé au Cameroun 2 essais versus la souche RUN 3598 (III-29)
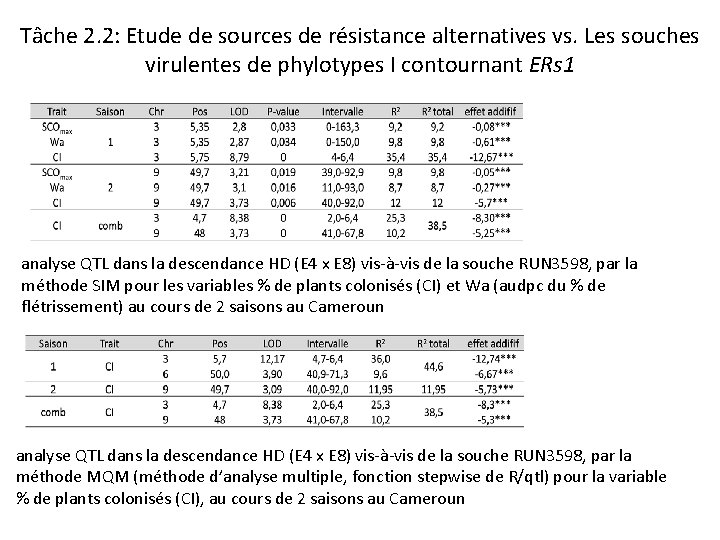
Tâche 2. 2: Etude de sources de résistance alternatives vs. Les souches virulentes de phylotypes I contournant ERs 1 analyse QTL dans la descendance HD (E 4 x E 8) vis-à-vis de la souche RUN 3598, par la méthode SIM pour les variables % de plants colonisés (CI) et Wa (audpc du % de flétrissement) au cours de 2 saisons au Cameroun analyse QTL dans la descendance HD (E 4 x E 8) vis-à-vis de la souche RUN 3598, par la méthode MQM (méthode d’analyse multiple, fonction stepwise de R/qtl) pour la variable % de plants colonisés (CI), au cours de 2 saisons au Cameroun

Tâche 2. 3: Production de descendances de lignées fixées par haplodiploïdisation en vue de recher des QTL de résistance à ces souches virulentes • Fourniture des semences de plantes HD par l’INRA-GAFL: bilan Ø 135 HD (E 8 x E 4) au CIRAD-Réunion Ø 135 HD (E 8 x E 4) à Technisem-Cameroun Ø 225 HD (E 8 x E 3) au CIRAD-Réunion Ø population HD (E 8 x E 9) disponible 2017

DISCUSSION sur l’ACTION 2 • Dissection résistance AG 91 -25 / 9 souches couvrant la diversité de la bactérie (thèse Salgon) ü Gène majeur ERs 1 spécifique de souches du phylotype I, contourné par des souches virulentes appartenant à tous les phylotypes testés ü Identification de 2 autres QTLs conférant des résistances partielles à des souches appartenant à tous les phylotypes, sauf le IIB Article publié dans Frontiers in Plant Science: Salgon et al, 2017, « Eggplant resistance to the Ralstonia solanacearum species complex involves both broadspectrum and strain-specific quantitative trait loci” ü Pas de détection de ERs 1 ni d’aucun QTL vs RUN 3598 (III-29) au Cameroun dans cette pop RILs (E 8 x E 6)

ACTION 2: Perspectives • Académique: clonage du gène majeur ERs 1 Ø Exploration de la diversité de l’aubergine pour la résistance et recherche d’éventuelles formes alléliques du gène Ø Etude du spectre d’efficacité de ERS 1 dans une collection de souches représentatives • Poursuite de la recherche de gènes/QTLs majeurs complémentaires d’ERs 1 et contrôlant les souches virulentes dans les populations HD créées pendant le projet • Sélection: développement de marqueurs étroitement liés au gène ERs 1 et aux QTLs EBWR 2 et EBWR 5 pour leur exploitation en SAM et leur transfert dans des fonds génétiques d’intérêt

Action 3: Suivi de la durabilité du gène ERs 1 Tâche 3. 1: Impact de la résistance de E 6 (Ers 1+QTLs) sur la structuration génétique d’une population parcellaire de Ralstonia solanacearum CIRAD-Réunion Tâche 3. 2: Diversité et contraintes évolutives sur les gènes candidats d’avirulence sur aubergine Tâche 3. 3: Validation fonctionnelle de l’avirulence CIRAD-Réunion, INRA-LIPM Toulouse, Virginia. Tech
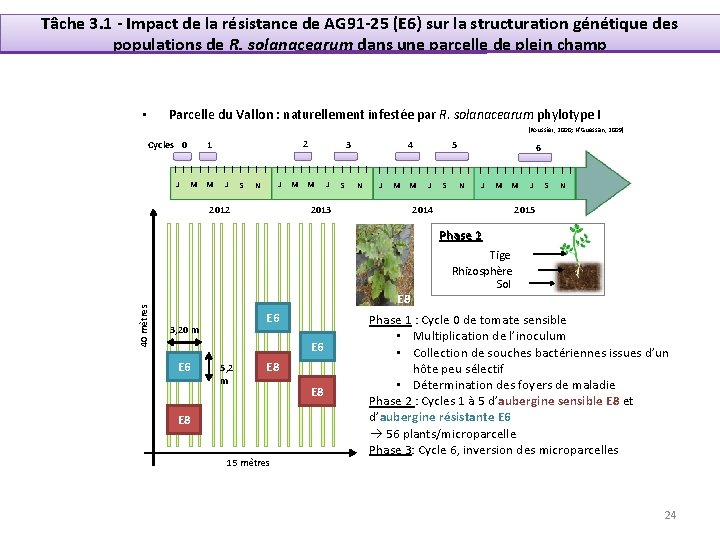
Tâche 3. 1 - Impact de la résistance de AG 91 -25 (E 6) sur la structuration génétique des populations de R. solanacearum dans une parcelle de plein champ Parcelle du Vallon : naturellement infestée par R. solanacearum phylotype I • (Poussier, 2000; N’Guessan, 2009) Cycles 0 J 2 1 M M J S J N 2012 M 3 M J S 5 4 N J M M J S 6 N J M M 2014 2013 J S N 2015 40 mètres Phase 12 E 6 E 8 E 6 3, 20 m E 6 5, 2 m E 8 15 mètres E 8 Tige Rhizosphère Sol Phase 1 : Cycle 0 de tomate sensible • Multiplication de l’inoculum • Collection de souches bactériennes issues d’un hôte peu sélectif • Détermination des foyers de maladie Phase 2 : Cycles 1 à 5 d’aubergine sensible E 8 et d’aubergine résistante E 6 56 plants/microparcelle Phase 3: Cycle 6, inversion des microparcelles 24
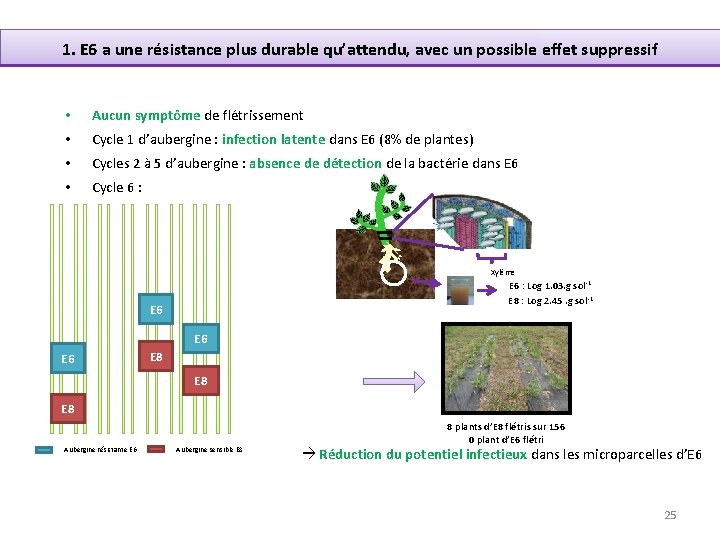
1. E 6 a une résistance plus durable qu’attendu, avec un possible effet suppressif • Aucun symptôme de flétrissement • Cycle 1 d’aubergine : infection latente dans E 6 (8% de plantes) • Cycles 2 à 5 d’aubergine : absence de détection de la bactérie dans E 6 • Cycle 6 : Xylème E 6 : Log 1. 03. g sol-1 E 8 : Log 2. 45. g sol-1 E 6 E 6 E 8 E 8 Aubergine résistante E 6 Aubergine sensible E 8 8 plants d’E 8 flétris sur 156 0 plant d’E 6 flétri Réduction du potentiel infectieux dans les microparcelles d’E 6 25
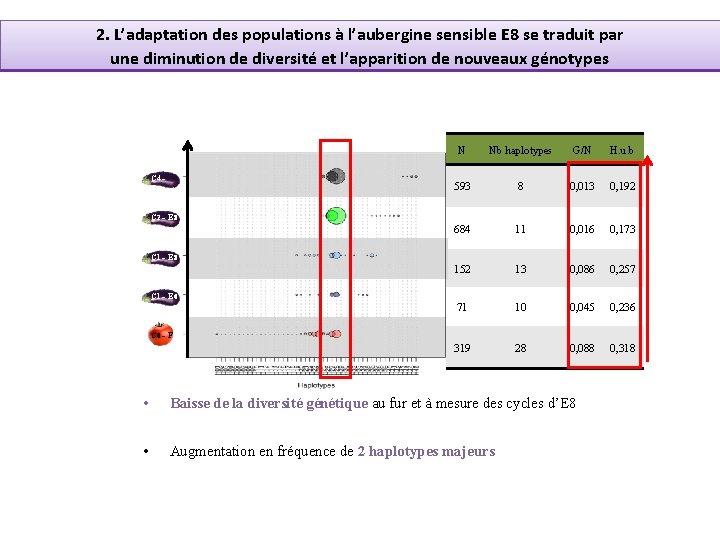
2. L’adaptation des populations à l’aubergine sensible E 8 se traduit par une diminution de diversité et l’apparition de nouveaux génotypes C 4 – E 8 N Nb haplotypes G/N H. u. b 593 8 0, 013 0, 192 684 11 0, 016 0, 173 152 13 0, 086 0, 257 71 10 0, 045 0, 236 319 28 0, 088 0, 318 C 2 – E 8 C 1 – E 6 C 0 – F • Baisse de la diversité génétique au fur et à mesure des cycles d’E 8 • Augmentation en fréquence de 2 haplotypes majeurs
Tâche 3. 1 - Conclusions • Le nouveau schéma MLVA-7 est adapté à des études de génétique des populations à l’échelle parcellaire – Article: Guinard J, Latreille A, Guérin F, Poussier S, Wicker E. 21 th December 2016 2017. New Multilocus Variable-Number Tandem -Repeat Analysis (MLVA) Scheme for Fine-Scale Monitoring and Microevolution-Related Study of Ralstonia pseudosolanacearum Phylotype I Populations. Appl Environ Microbiol. 83(5): e 03095 -03016. • L’aubergine E 6 reste résistante après 5 cycles de culture • La résistance d’E 6 induit une chute du potentiel infectieux du sol • L’aubergine sensible E 8 impacte la diversité et de la structure génétique des populations bactériennes, en sélectionnant un nombre restreint d’haplotypes
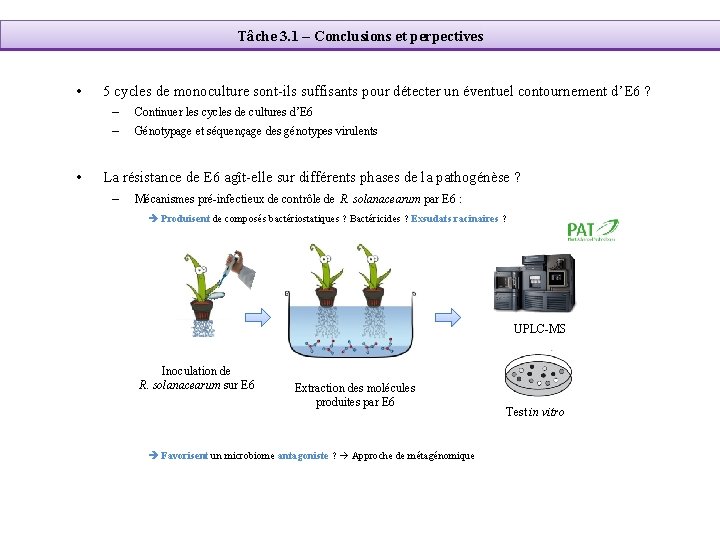
Tâche 3. 1 – Conclusions et perpectives • • 5 cycles de monoculture sont-ils suffisants pour détecter un éventuel contournement d’E 6 ? – Continuer les cycles de cultures d’E 6 – Génotypage et séquençage des génotypes virulents La résistance de E 6 agît-elle sur différents phases de la pathogénèse ? – Mécanismes pré-infectieux de contrôle de R. solanacearum par E 6 : Produisent de composés bactériostatiques ? Bactéricides ? Exsudats racinaires ? UPLC-MS Inoculation de R. solanacearum sur E 6 Extraction des molécules produites par E 6 Favorisent un microbiome antagoniste ? Approche de métagénomique Test in vitro
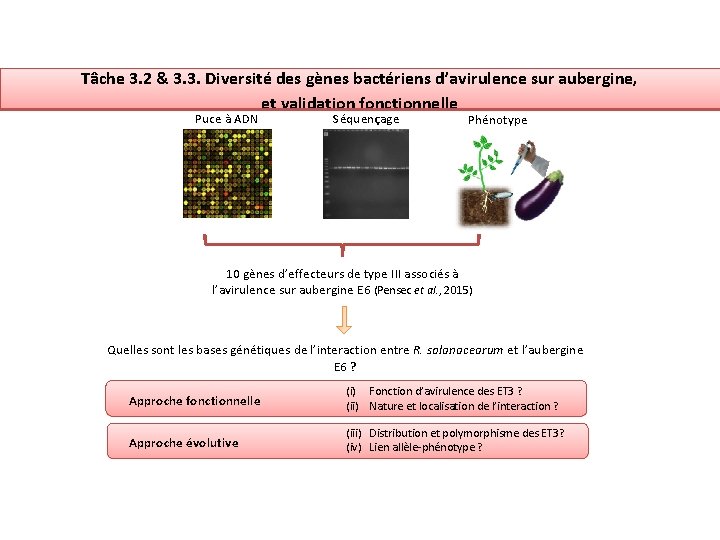
Tâche 3. 2 & 3. 3. Diversité des gènes bactériens d’avirulence sur aubergine, et validation fonctionnelle Puce à ADN Séquençage Phénotype 10 gènes d’effecteurs de type III associés à l’avirulence sur aubergine E 6 (Pensec et al. , 2015) Quelles sont les bases génétiques de l’interaction entre R. solanacearum et l’aubergine E 6 ? Approche fonctionnelle (i) Fonction d’avirulence des ET 3 ? (ii) Nature et localisation de l’interaction ? Approche évolutive (iii) Distribution et polymorphisme des ET 3? (iv) Lien allèle-phénotype ?
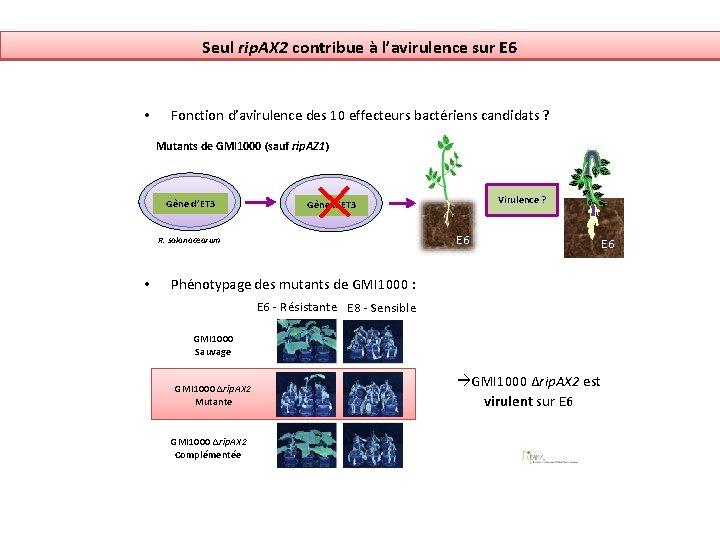
Seul rip. AX 2 contribue à l’avirulence sur E 6 • Fonction d’avirulence des 10 effecteurs bactériens candidats ? Mutants de GMI 1000 (sauf rip. AZ 1) Gène d’ET 3 E 6 R. solanacearum • E 6 Virulence ? E 6 Phénotypage des mutants de GMI 1000 : E 6 - Résistante E 8 - Sensible GMI 1000 Sauvage GMI 1000 ∆rip. AX 2 Mutante GMI 1000 ∆rip. AX 2 Complémentée GMI 1000 ∆rip. AX 2 est virulent sur E 6
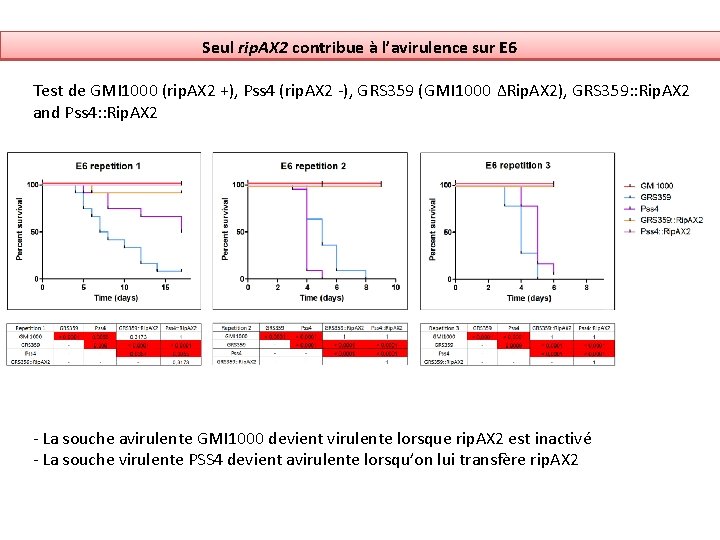
Seul rip. AX 2 contribue à l’avirulence sur E 6 Test de GMI 1000 (rip. AX 2 +), Pss 4 (rip. AX 2 -), GRS 359 (GMI 1000 ΔRip. AX 2), GRS 359: : Rip. AX 2 and Pss 4: : Rip. AX 2 - La souche avirulente GMI 1000 devient virulente lorsque rip. AX 2 est inactivé - La souche virulente PSS 4 devient avirulente lorsqu’on lui transfère rip. AX 2
Le contrôle de Rip. AX 2 semble localisé dans la base de tige
Distribution et polymorphisme de rip. AX 2 Distribution variable de rip. AX 2 • Phylotypes Absent Présent Total % Présence I 4 62 66 93% AFRIQUE – ASIE 1 50 51 98% AMERIQUE DU SUD 3 9 12 75% IIA 5 4 9 44% IIB 7 3 10 30% III 2 4 6 66% Total 18 73 91 82, 4% Majoritairement présent dans le phylotype I Majoritairement présent en Afrique et en Asie rip. AX 2 est polymorphe : 26 allèles • Nb allèles Protéine 0 Avirulente Virulente Total général ABSENTE 7 10 18 13 OK 31 8 57 13 TRONQUEE 9 4 16 47 22 91 Total général Allèle GMI 1000 Protéine OK Souches phénotypées sur E 6 Avirulente Virulente Total général 25 5 44 13 allèles produisant chacune protéine tronquée L’allèle Rip. AX 2 GMI 1000 est dominant (44 souches) : - souches avirulentes (25) - souches virulentes (5)

Distribution et polymorphisme de rip. AX 2 • Un allèle dominant: Rip. AX 2 GMI 1000 (60. 3%) • Present chez I, IIA, IIB • Richesse allélique : Asie (8 allèles) > Afrique (7 allèles) > Amérique du Sud (4 allèles) > Indian Ocean (1) • 13 allèles correspondent à des protéines tronquées (< 80% de la protéine Rip. AX 2 chez GMI 1000)

DISCUSSION sur l’ACTION 3 • Absence de contournement de la résistance d’E 6 jusqu’au cycle 5 Ø Passer en conditions contrôlées? • E 6 semble avoir plusieurs mécanismes de résistance agissant sur plusieurs phases de la pathogénèse: – Réduction du potentiel infectieux : mécanisme diminuant l’infection » Biochimie et métagénomique comparative de la rhizosphère? – Reconnaissance de Rip. AX 2 après pénétration dans les racines » Protéines végétales impliquées ?

DISCUSSION sur l’ACTION 3 • rip. AX 2: gène effecteur bactérien impliqué dans la résistance E 6 vs GMI 1000 Ø Reconnaissance spécifique ERs 1/rip. AX 2? • Contrôle de GMI 1000 au niveau de la zone hypocotylaire • Gène présent dans le phylotype I, IIA, IIB, III (80% des 91 souches testées) Ø Souches du phylotype IV? • 26 allèles rip. AX 2 identifiés dont une version très majoritaire (60%) correspondant à celle de GMI 1000 Ø Etendre le dispositif expérimental à un échantillon plus représentatif pour confirmer la présence majoritaire • L’existence d’une association allèle/phénotype sur E 6 est à affiner Ø Séquences régulatrices, environnements géniques, épigénétiques …? Un article à soumettre dans Frontiers in Plant science: Morel A. et al 2017
- Slides: 36