mutazioni puntiformi Vincenzo Nigro Dipartimento di Patologia Generale

























- Slides: 37

mutazioni puntiformi Vincenzo Nigro Dipartimento di Patologia Generale Seconda Università degli Studi di Napoli Telethon Institute of Genetics and Medicine (TIGEM)

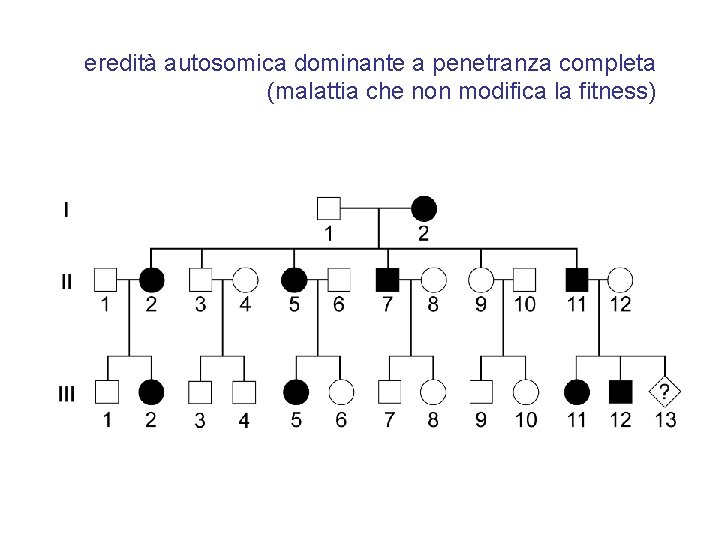
Malattie genetiche da mutazione in 1 allele Le mutazioni monoalleliche possono causare disordini a trasmissione dominante o recessiva legata all’X negli uomini • • • Se la malattia a trasmissione dominante è grave in età fertile e pertanto limita o annulla la capacità riproduttiva (bassa fitness), le mutazioni monoalleliche sono nuove e spesso distribuite in modo casuale Se la malattia dominante non è grave in età fertile e non limita in alcun modo la capacità riproduttiva (normale fitness), le mutazioni monoalleliche sono ereditate da un genitore e spesso si tramandano da molte generazioni Se la malattia è recessiva legata all’X ed è letale ha una vita media di tre generazioni, perché le donne trasmettono gli alleli mutati in eterozigosi e gli uomini li eliminano

eredità autosomica dominante a penetranza completa (malattia che non modifica la fitness)

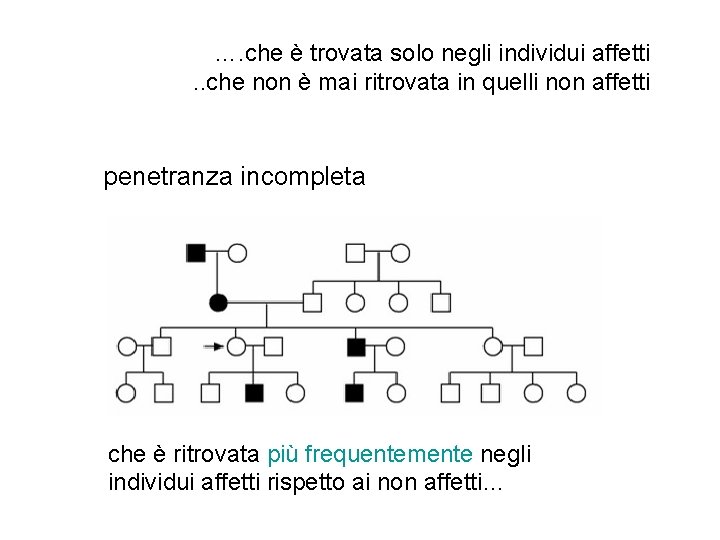
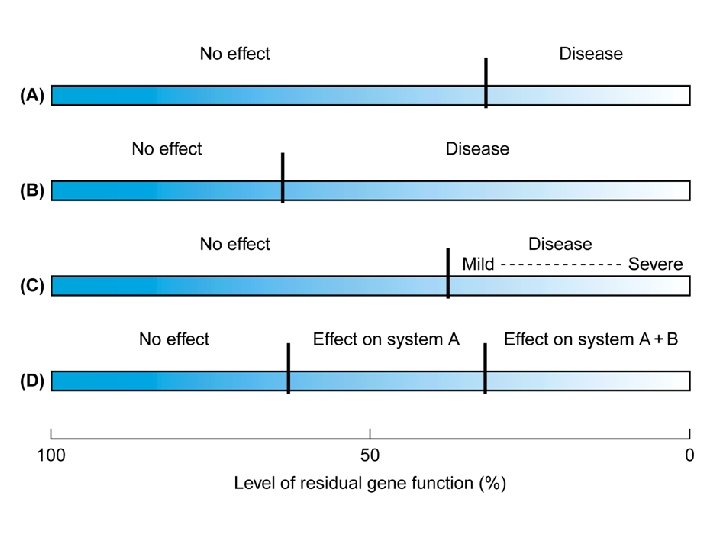
Cos’è una mutazione causativa? Una variazione della sequenza del DNA …. • . . che è trovata solo negli individui affetti • . . che non è mai ritrovata in quelli non affetti • . . che spiega il processo patologico • . . che, quando corretta per tempo, fa recuperare un fenotipo normale

…. che è trovata solo negli individui affetti. . che non è mai ritrovata in quelli non affetti penetranza incompleta che è ritrovata più frequentemente negli individui affetti rispetto ai non affetti…

sostituzioni • le sostituzioni sono indicate dal carattere “>”. Ad esempio, 76 A>C indica che in posizione 76 un’adenina è sostituita da una citosina 88+1 G>T (oppure IVS 2+1 G>T) indica che una guanina è sostituita da una timina in posizione +1 dell’introne 2, posizionato tra i nucleotidi 88 e 89 del c. DNA 89 -2 A>C (oppure IVS 2 -2 A>C) indica che un’adenina è sostituita da una citosina in posizione -2 dell’introne 2, posizionato tra i nucleotidi 88 e 89 del c. DNA


Numerazione dei nucleotidi Nucleotidi del c. DNA • Il nucleotide +1 è la A dell’ ATG-codone di inizio della traduzione • Il nucleotide che precede al 5' l’ATG-codone di inizio della traduzione è denominato -1; non esiste una base 0 • Il nucleotide che segue al 3' il codone di terminazione è denominato *1


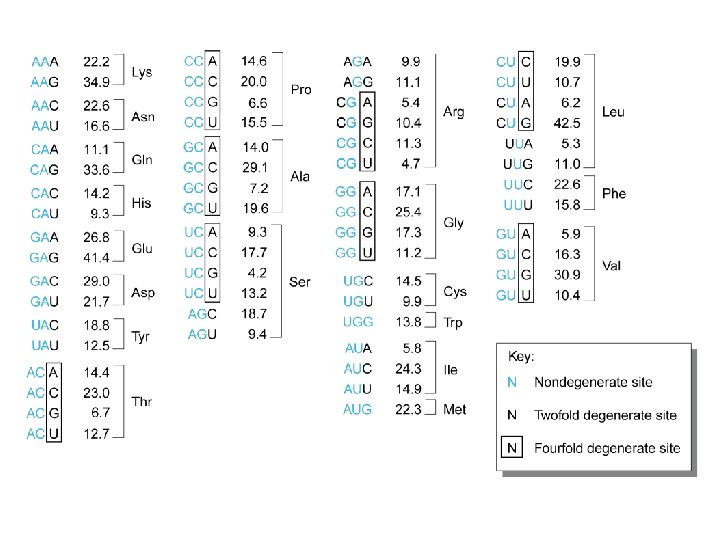
mutazioni SNPs teoricamente previste T>A o G , C>G or A G>T o C , A>T or G trasversioni transizioni T>C, C>T, G>A, A>G 46, 000 trasversioni transizioni 12, 000 trasversioni transizioni SEA 3057

Il meccanismo più comune di mutazione NH 2 H 3 C N Cytosine H 3 C N N O O metilazione N O deaminazione 5 -methylcytosine CG CG NH TG CA N O Thymine


mutazioni puntiformi missenso • Le mutazioni missenso sono quelle in cui il cambiamento determina nel prodotto proteico la sostituzione di un aminoacido con un aminoacido differente • Sebbene queste alterazioni generalmente non provochino conseguenze nella funzionalità della proteina (polimorfismi o varianti) , ci sono casi in cui anche una minima alterazione può avere conseguenze gravi

acrocefalosindattilia sindrome di Apert • 1: 65. 000 alla nascita • craniosinostosi, volta cranica a forma conica • ipertensione endocranica • ritardo mentale • ipoplasia della parte centrale della faccia • sindattilia delle dita delle mani e dei piedi • sordità e atrofia ottica

acrocefalosindattilia sindrome di Apert • tutti i pazienti hanno la stessa mutazione Apert (Cys 755 Gly) del gene human fibroblast growth factor receptor 2 (FGFR 2) • la mutazione è in eterozigosi • de novo • cromosoma 10 q 26 • la sindrome è allelica con Crouzon e Pfeiffer

sindrome di Pfeiffer • alcuni pazienti hanno la mutazione Pfeiffer (Cys 342 Arg) del gene human fibroblast growth factor receptor 2 (FGFR 2) • altri la mutazione Pro 252 Arg in FGFR 1 • la mutazione è in eterozigosi • de novo • cromosoma 10 q 26 • la sindrome è allelica con Crouzon e Apert

disostosi cranio facciale sindrome di Crouzon • alcuni pazienti hanno la mutazione (Cys 342 Tyr) del gene human fibroblast growth factor receptor 2 (FGFR 2) • la mutazione è in eterozigosi • de novo • cromosoma 10 q 26 • la sindrome è allelica con Pfeiffer e Apert con alcune mutazioni in comune

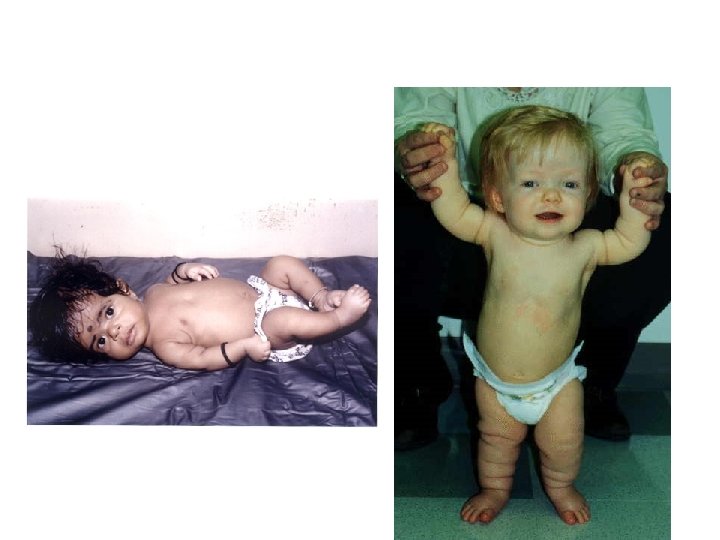
acondroplasia • • nanismo dismorfico (1: 35. 000) arti corti e testa sproporzionatamente più grossa fronte prominente e naso appiattito altezza media 130 cm nei maschi 125 cm nelle femmine • La mutazione è in eterozigosi • Gly 380 Arg nel recettore 3 del "fibroblast growth factor" (FGFR 3) a 4 p 16. 3 • autosomico dominante a penetranza completa

acondroplasia • La mutazione conferisce una funzione aumentata al recettore dell'FGF (allele ipermorfo) che è una tirosinchinasi di membrana • In risposta all'FGF il recettore dimerizza e si fosforila trasducendo un segnale con la funzione di rallentare la proliferazione dei condrociti e quindi la crescita ossea • Topi senza il gene FGF 3 R hanno ossa lunghe e vertebre allungate


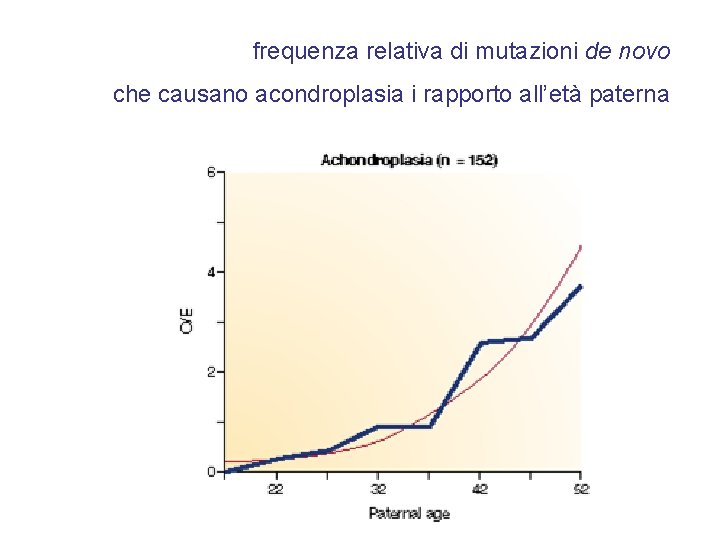
frequenza relativa di mutazioni de novo che causano acondroplasia i rapporto all’età paterna

numero di divisioni nelle linea germinale maschile


ipocondroplasia • L'ipocondroplasia ha caratteristiche simili all'acondroplasia, ma di gravità minore con un coinvolgimento craniofacciale inferiore. L'altezza può risultare ai limiti della norma e la malattia viene spesso non diagnosticata. • L'ipocondroplasia è meno omogenea: circa il 70% dei casi è dovuto alla sostituzione N 540 K del gene FGFR 3, mentre non si conosce la mutazione nel restante 30%.

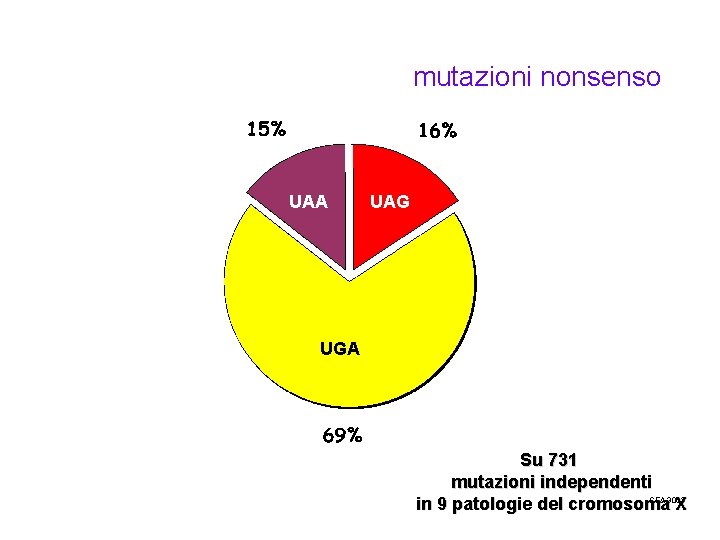
mutazioni puntiformi nonsenso • La mutazione nonsenso è quella in cui la modificazione nucleotidica provoca la creazione di un tripletta di stop, che blocca la sintesi della proteina prematuramente. • In questo caso, la funzionalità della proteina dipenderà dalla posizione dello stop.

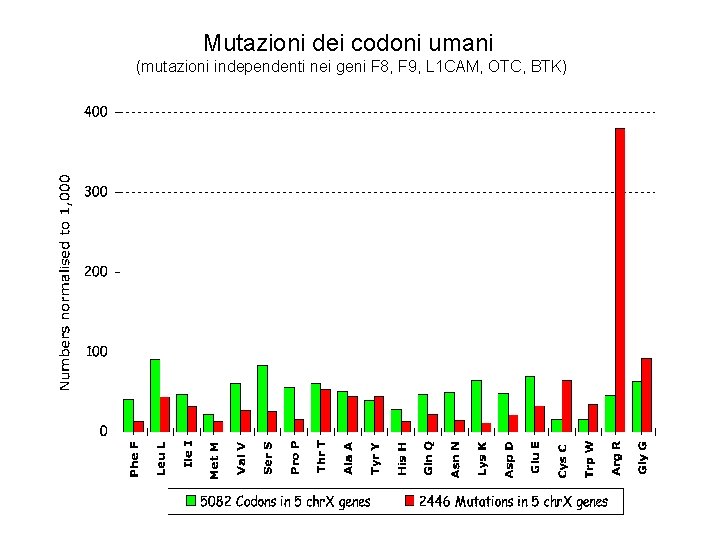
Mutazioni dei codoni umani (mutazioni independenti nei geni F 8, F 9, L 1 CAM, OTC, BTK)

mutazioni nonsenso UAA UAG UGA Su 731 mutazioni independenti SEA 3063 in 9 patologie del cromosoma X

mutazioni frame-shift • Le mutazioni frame-shift o di slittamento del modulo di lettura consistono nell’inserzione o delezione di un numero di nucleotidi non divisibile per 3 (1, 2, 4, 5, 7, 8, 10, ecc. ) conseguente sfasamento della cornice di lettura delle triplette dell'RNA messaggero. • Questa mutazione determina la traduzione non corretta della proteina a valle della mutazione.

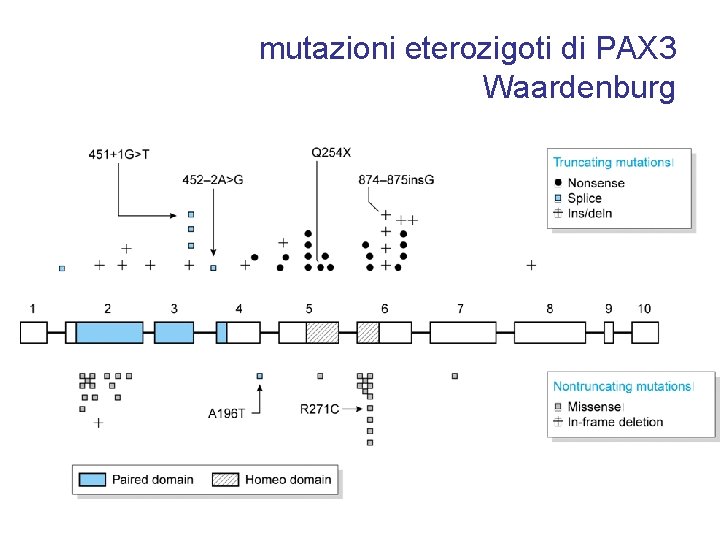
mutazioni eterozigoti di PAX 3 Waardenburg

mutazioni eterozigoti di PAX 3 Waardenburg • sordità (o deficit uditivo di vario livello) bilaterale, • modifiche nella pigmentazione, sia dei capelli (albinismo parziale, in genere piebaldismo) che della pelle, • anomalie nello sviluppo dei tessuti derivati dalla cresta neurale • lateralizzazione del canto mediale • diverso colore degli occhi (eterocromia), di solito uno marrone e l'altro blu


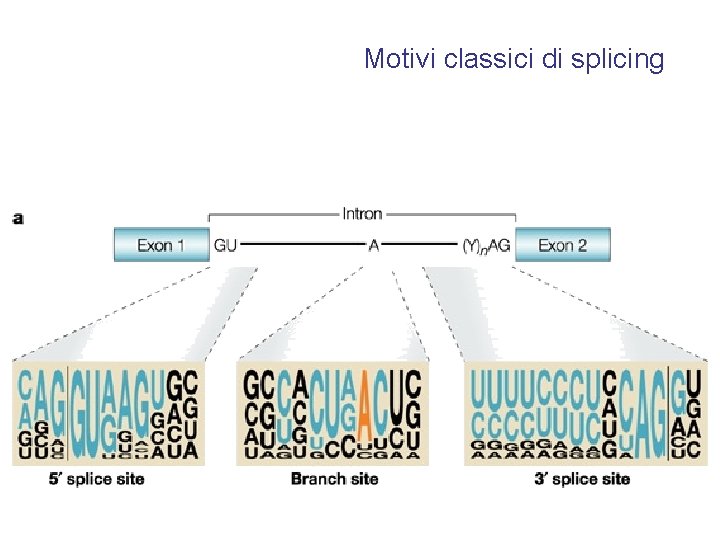
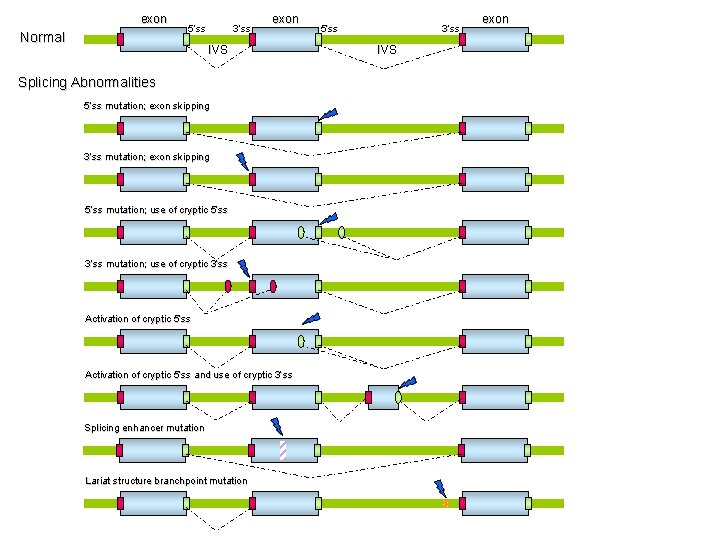
Motivi classici di splicing

exon Normal 5’ss 3’ss exon IVS Splicing Abnormalities 5’ss mutation; exon skipping 3’ss mutation; exon skipping 5’ss mutation; use of cryptic 5’ss 3’ss mutation; use of cryptic 3’ss Activation of cryptic 5’ss and use of cryptic 3’ss Activation of cryptic 5’ss Splicing enhancer mutation Lariat structure branchpoint 5’ss 3’ss IVS exon

Progeria Hutchinson-Gilford • invecchiamento precoce • bassa statura, pelle rugosa • calvizie, assenza di tessuto adiposo • aterosclerosi ed infarto

Progeria Hutchinson-Gilford • nuova mutazione in eterozigosi del gene lamina A • la mutazione è in eterozigosi • de novo • cromosoma 1 q 23 • La mutazione non cambia l'aminoacido glicina G 608 G, ma introduce un sito donor di splicing GGT che fa perdere 50 aminoacidi alla proteina • sperimentazione con inibitori di farnesil-trasferasi

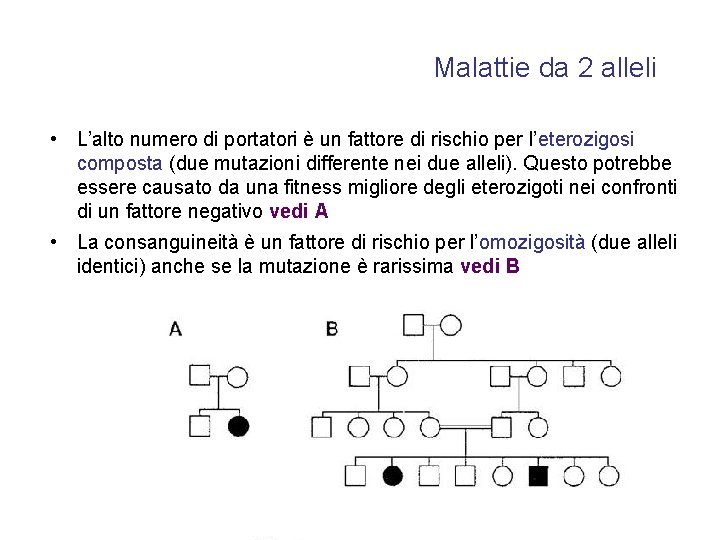
Malattie genetiche da mutazione in 2 alleli Le mutazioni bialleliche possono causare disordini a trasmissione autosomica recessiva • • • Se la malattia a trasmissione recessiva è grave in età fertile e limita o annulla la capacità riproduttiva (bassa fitness), le mutazioni non si estinguono comunque perché i portatori sani sono 10 -10. 000 volte più numerosi degli affetti Le mutazioni in genere si trasmettono da 100 -1000 generazioni, mentre le nuove mutazioni sono rare Solo se la malattia è biallelica le mutazioni hanno una firma etnica che caratterizza una località di origine e un fondatore comune eterozigote sano

Malattie da 2 alleli • L’alto numero di portatori è un fattore di rischio per l’eterozigosi composta (due mutazioni differente nei due alleli). Questo potrebbe essere causato da una fitness migliore degli eterozigoti nei confronti di un fattore negativo vedi A • La consanguineità è un fattore di rischio per l’omozigosità (due alleli identici) anche se la mutazione è rarissima vedi B
 Nigro & nigro pc
Nigro & nigro pc Mutazioni puntiformi
Mutazioni puntiformi Mutazioni puntiformi
Mutazioni puntiformi Campo elettrico fisica
Campo elettrico fisica Teamwork poems that rhyme
Teamwork poems that rhyme Mazzoldi nigro voci meccanica e termodinamica
Mazzoldi nigro voci meccanica e termodinamica Mutazioni genetiche
Mutazioni genetiche Poliploidia
Poliploidia Mutazioni genetiche
Mutazioni genetiche Mutazione genica
Mutazione genica Mutazioni somatiche e germinali
Mutazioni somatiche e germinali Poliglutammina
Poliglutammina Mutazioni
Mutazioni Cromosomi bilanciatori
Cromosomi bilanciatori Patologia vegetale molecolare
Patologia vegetale molecolare Patologia usac
Patologia usac Neoplasia
Neoplasia Hemolinfatica
Hemolinfatica Patologia sociale
Patologia sociale Hemoptisis
Hemoptisis Patologia ficatului
Patologia ficatului Patologia
Patologia Corporeale
Corporeale Nablacion
Nablacion Neuropatia metabolica
Neuropatia metabolica Patologia sociale
Patologia sociale Hospedero definitivo de hymenolepis nana
Hospedero definitivo de hymenolepis nana Infarto renal
Infarto renal Onfalocelo
Onfalocelo Q es la patologia
Q es la patologia Pattern recognition unibo
Pattern recognition unibo Patologia
Patologia Hiv patologia
Hiv patologia Infarto subendocárdico
Infarto subendocárdico Patologia
Patologia Informe de patología estructural
Informe de patología estructural Dot resposta
Dot resposta Ic monti pollenza
Ic monti pollenza