MUTANTS HEPATITE B MJ Carles RHEVIR 2005 MUTANTS
MUTANTS HEPATITE B M-J Carles RHEVIR 2005

MUTANTS HEPATITE B q Erreur de réplication de la RT q Utilisation de l’interféron q Il existe Mutants « S » q Il existe Mutants sur gène P q Il existe Mutants X-préX
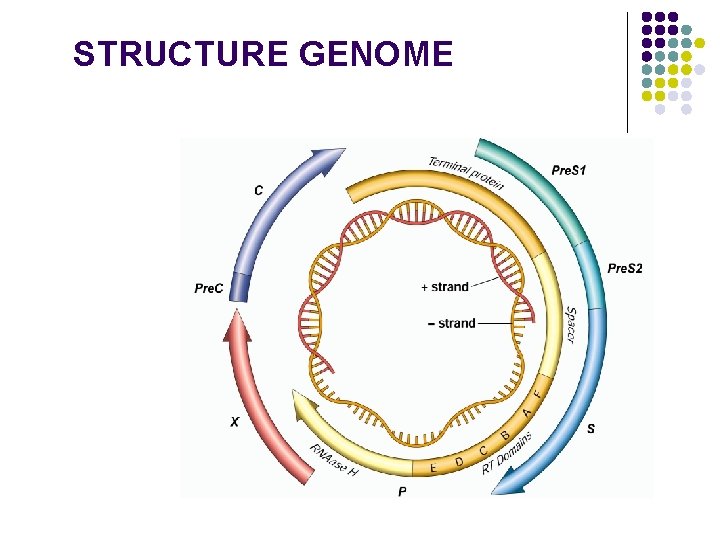
STRUCTURE GENOME

MUTANTS HEPATITE B l l Mutants spontanés dus aux erreurs de la RT Pression de sélection : l Réponse Immune spontanée: mutants C-préC l Réponse immune induite par vaccination ou transmission passive d ’anti-Hbs l Traitements utilisant analogues nucléosidiques ou nucléotidiques de la polymérase

MUTANTS HEPATITE B x Erreur q de réplication de la RT Utilisation de l’interféron x Il existe Mutants « S » x Il existe Mutants sur gène P q Il existe Mutants X-préX

MUTANTS « S » q Modification structurale de l’Ag. HBS q Mutants dus à pression de sélection q Ag. HBs négatif q Anti-Hbc positif q ADN négatif

MUTANTS « S » l l l Ag. HBs = protéine de 226 aa déterminant antigénique majeur: déterminant « a » position 124 à 147 Mutations les plus fréquentes: l l l F 134 M 133 D 144 G 145 R 144 et 145 connues pour être associées à échappement au Ig ou vaccin
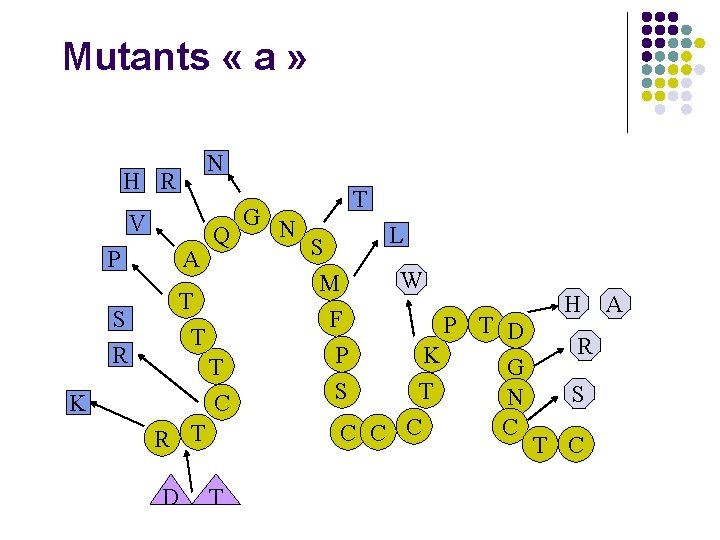
Mutants « a » N H R V P S R A G N Q T T T C K R T D T T S M F P S L W H P T D R K G T S N C C T C A

MUTANTS « S » l Variants « S » émergent sous effet de pression de sélection: l l Réponse immunitaire naturelle Réponse induite par vaccination Action thérapeutique: Ig ou lamivudine Variants décrits chez: l l Enfants vaccinés Transplantés hépatiques ayant reçu des Ig Porteurs chroniques à infection occulte Porteurs chroniques traités par lamivudine

MUTANTS « S » l l Surtout étudiés en Asie et Afrique prévalence 2 à 28% Espagne: 16%: Eschevaria 2005 France: 55 séquences (Paul Brousse): l 31 substitutions dans région hydrophile(56%) § 134: 7 133: 6 144: 6 145: 6 § 16 patients (29%) : mutations entraînant modification propriétés physico-chimiques donc défaut diagnostic § A. M Roque-Afonso path bio juin 2005

Diagnostic mutants « S » l problème de détection par techniques de dépistage : Ac dirigés contre région hydrophile et en particulier « a » l meilleure approche: mélange d ’Ac monoclonaux l Recherche de l’ADN viral l Présence simultanée de L ’Ac et L ’Ag Hbs

MUTANTS S x Modification x Ag. HBs négatif ou positif x Anti-Hbc q structurale de l’Ag. HBS positif ADN négatif

Mutants C/ pré-C q N’expriment plus Ag. HBc dans les hépatocytes q Mutants de résistance à l’interféron q Ag. HBe positif q Anti-HBe négatif q ADN B positif

Mutants C/ pré-C l l Mutation pré-C: codon stop: Absence de synthèse d ’Ag Hbe Mutations dans région BCP: Diminution de synthèse de l ’Ag Hbe Présence d ’anti-Hbe Persistance d ’une réplication virale: § § § ADN positif Transaminases élevées Progression de la maladie hépatique
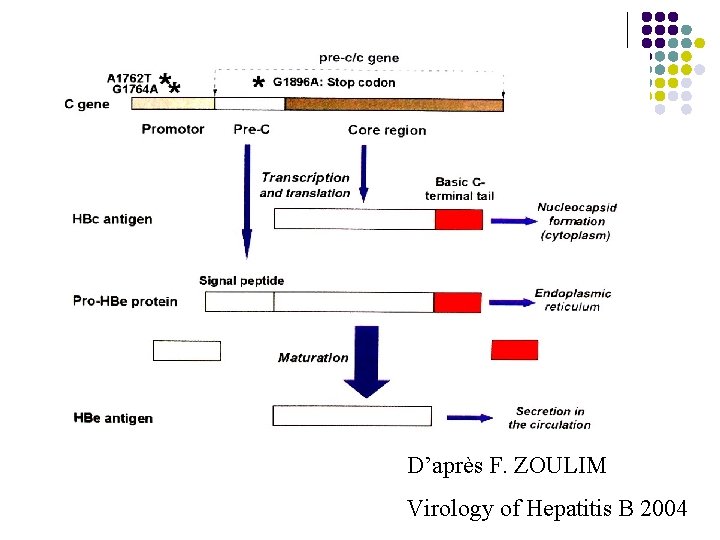
D’après F. ZOULIM Virology of Hepatitis B 2004

Mutants C/ pré-C l Plusieurs profils: l Réplication constante avec transaminases élevées l Réplication avec fluctuation des transaminases l Variations dans la réplication virale avec poussées cytolytiques et rémissions qui peuvent durer plusieurs mois

Mutants C/ pré-C l l l Prévalence: 22% il y a 10 ans, 43% a l ’heure actuelle Type de mutation dépendant du génotype Associés à des hépatites fulminantes Virus échappe à la réponse immune Plus fort risque d ’évolution vers la cirrhose A suivre par ADN et ALAT tous les 3 à 6 mois

Mutants C/ pré-C q N’expriment plus Ag. HBc dans les hépatocytes q Mutants de résistance à l’interféron q Ag. HBe positif q Anti-HBe négatif x ADN B positif

MUTATIONS DE RESISTANCE au traitement q Mutation sur le gêne C q Mutation sur le gêne P (polymérase) q Sont rares avec lamivudine q Résistance croisée entre différentes molécules q Mee par augmentation de la charge virale en suivi de traitement

Traitements l Interféron + peg –interféron l Analogues nucléosidiques: l l l Lamivudine : 3 TC Emtricitabine: Emtriva Adefovir: Hepsera Tenofovir: Viread clevudine entecavir
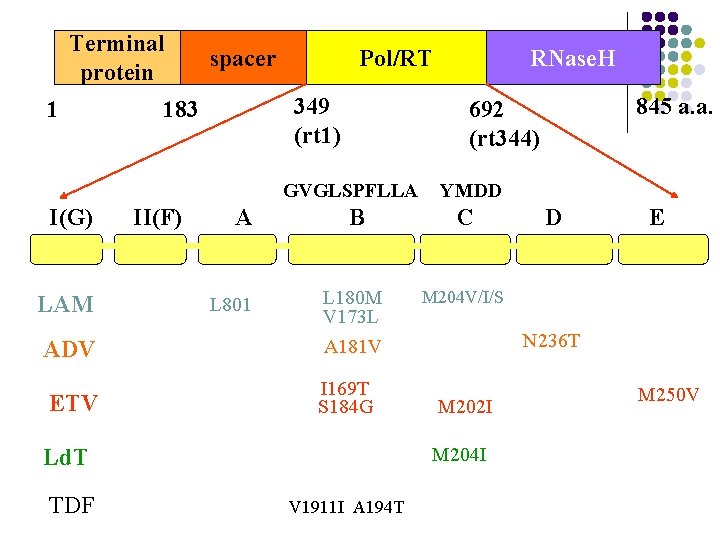
Terminal protein 1 spacer Pol/RT 349 (rt 1) 183 A YMDD B C M 204 V/I/S ADV L 180 M V 173 L A 181 V ETV I 169 T S 184 G LAM II(F) L 801 V 1911 I A 194 T D E N 236 T M 202 I M 204 I Ld. T TDF 845 a. a. 692 (rt 344) GVGLSPFLLA I(G) RNase. H M 250 V

l Domaine C contient motif YMDD= site catalytique de l ’enzyme l mutation YMDD : la + fréquente , mutation de résistance a la lamivudine, emtricitabine l Pas de résistance croisée entre les différents nucléosidiques et nucléotidiques

Incidence des résistances l Lamivudine: 24% en 1 an 70% en 4 ans l Adefovir 15% en 4 ans l ceci en monothérapie l Intérêt des bi ou trithérapie? ?

MUTATIONS DE RESISTANCE au traitement q Mutation sur le gêne C x Mutation sur le gêne P(polymérase) q Sont rares avec lamivudine q Résistance croisée entre différentes molécules x Mee par augmentation de la charge virale en suivi de traitement

CONCLUSION l Evolution permanente des techniques pour mee des virus qui échappent à réponse immune ou aux traitements l Importance de la biologie moléculaire dans le diagnostic de ces variants
- Slides: 25