Metodi per studiare lespressione dei geni Northern blot

Metodi per studiare l’espressione dei geni • • • Northern blot Trascrittasi Inversa -PCR (RT-PCR) Ibridazione In situ Trascrizione In vitro DNA Microarray

Purificazione dell’RNA • Procedura – Lisi delle cellule con un reagente che dissocia le nucleoproteine e inibisce la RNAsi – Rimozione delle proteine – Precipitazione specifica dell’RNA

Northern blot • Per determinare la dimensione e la quantita’ di specifici m. RNA • Studi sull’espressione genica

Northern blot – Elettroforesi dell’RNA in gel contenente formaldeide per mantenere l’RNA in forma completamente lineare – Trasferimento dell’RNA su una membrana – Ibridazione con una sonda marcata
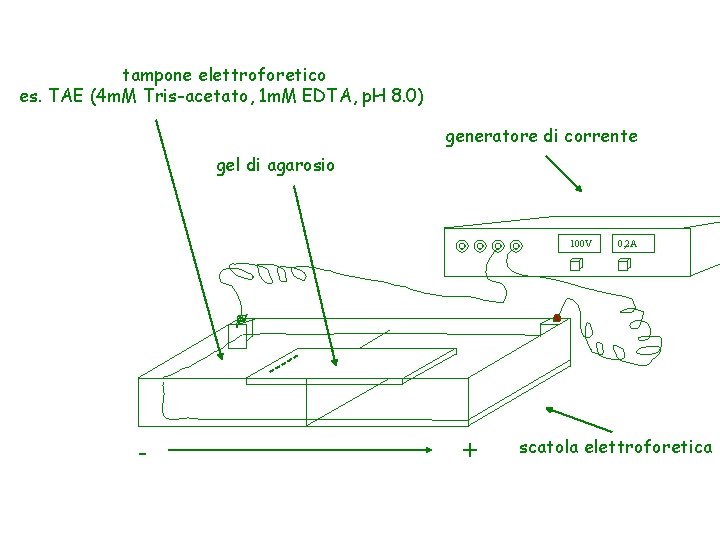
tampone elettroforetico es. TAE (4 m. M Tris-acetato, 1 m. M EDTA, p. H 8. 0) generatore di corrente gel di agarosio 100 V - + 0, 2 A scatola elettroforetica
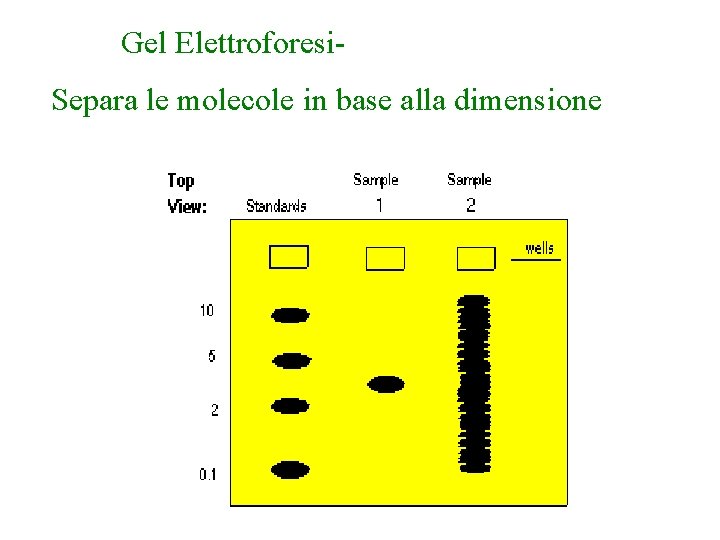
Gel Elettroforesi. Separa le molecole in base alla dimensione
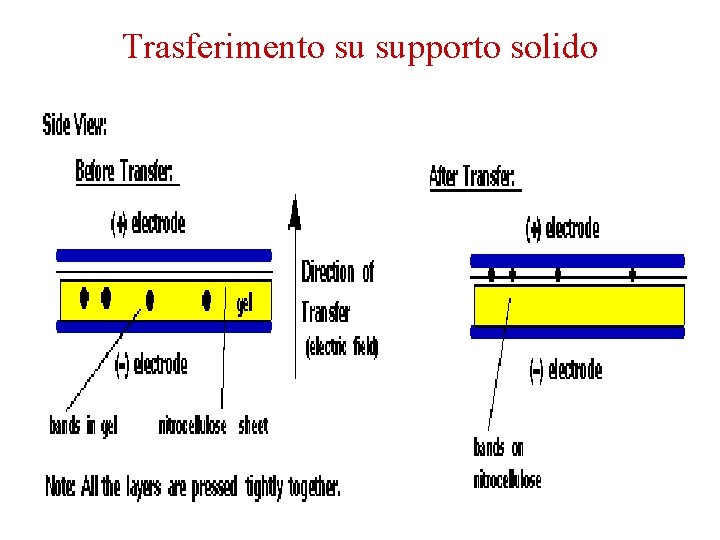
Trasferimento su supporto solido
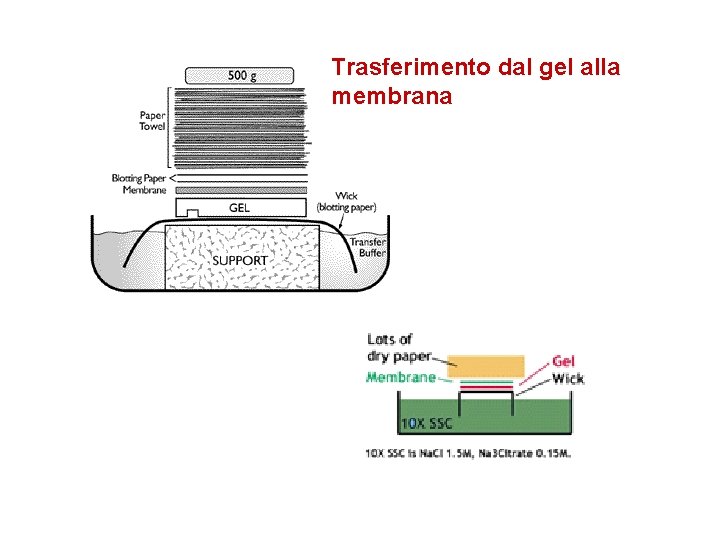
Trasferimento dal gel alla membrana
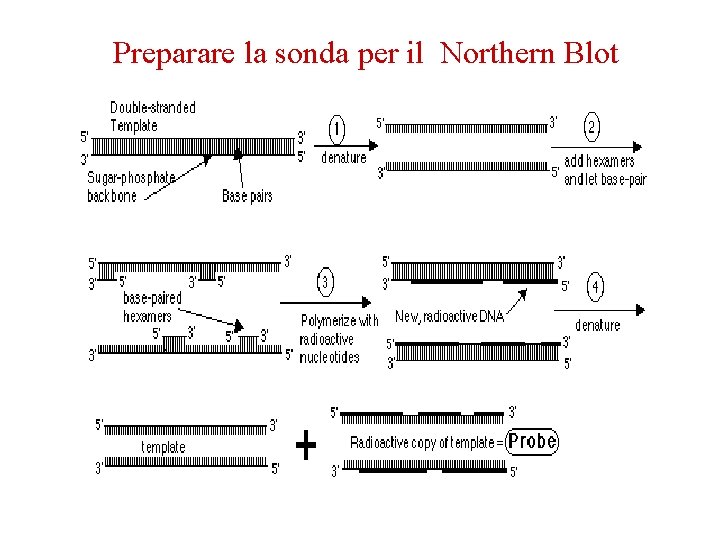
Preparare la sonda per il Northern Blot

Ibridazione • La sonda marcata e’ aggiunta ad una soluzione contenente il supporto solido che lega l’RNA da analizzare

Lavaggio • Rimozione della sonda non legata al supporto solido

Rivelazione degli ibridi • Esposizione di un film se la sonda e’ marcata radioattivamente • Se la sonda e’ marcata con un enzima si procede alla reazione enzimatica che produce colore direttamente sul supporto solido

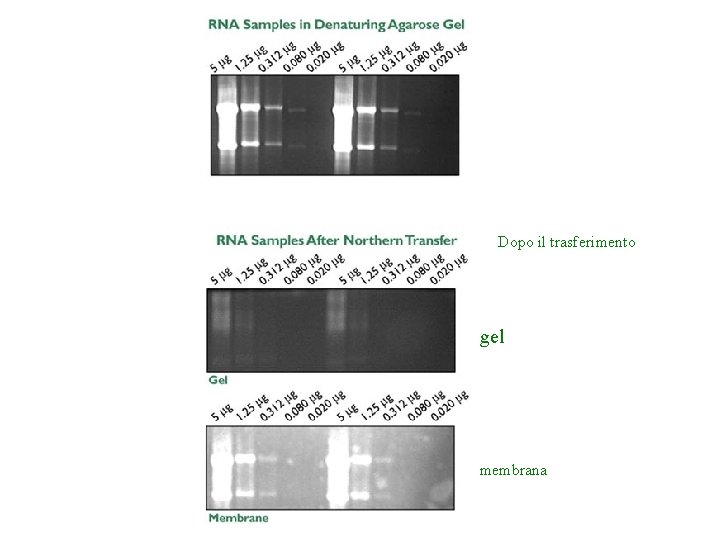
Dopo il trasferimento gel membrana

Northern blot • La rivelazione avviene usando: – DNA marcato con radioattivo(32 P) – DNA marcato con un enzima che catalizza una reazione che produce luce o colore
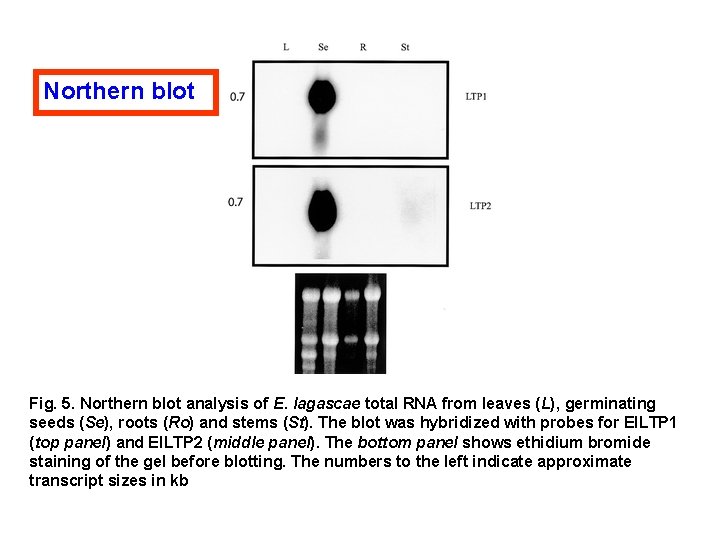
Northern blot Fig. 5. Northern blot analysis of E. lagascae total RNA from leaves (L), germinating seeds (Se), roots (Ro) and stems (St). The blot was hybridized with probes for El. LTP 1 (top panel) and El. LTP 2 (middle panel). The bottom panel shows ethidium bromide staining of the gel before blotting. The numbers to the left indicate approximate transcript sizes in kb

Svantaggi del Northern Blot • Richiede grandi quantita’ di RNA • E’ un processo lungo e laborioso

Trascrittasi Inversa-�PCR • Rivelazione di m. RNA molto rari • Analisi di RNA con pochissime quantita’

Procedura • Purificazione dell’RNA • Aggiungere i primer • mescolare RNA con la trascrittasi inversa per effettuare la sintesi del primo filamento di c. DNA • Aggiungere la DNA polimerasi termostabile per effettuare la sintesi del secondo filamento di c. DNA e per amplificarlo con i cicli della PCR
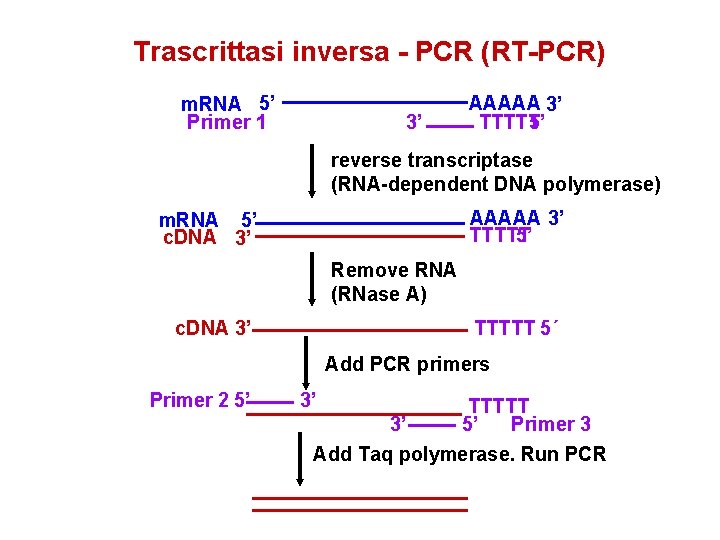
Trascrittasi inversa - PCR (RT-PCR) m. RNA 5’ Primer 1 3’ AAAAA 3’ TTTTT 5’ reverse transcriptase (RNA-dependent DNA polymerase) AAAAA 3’ 5’ TTTTT m. RNA 5’ c. DNA 3’ Remove RNA (RNase A) c. DNA 3’ TTTTT 5´ Add PCR primers Primer 2 5’ 3’ TTTTT 3’ 5’ Primer 3 Add Taq polymerase. Run PCR

Reverse transcriptase-PCR (= RT-PCR) Epoxide hydrolase + + - - - l 2027 1904 1584 947 831 564 l se r st pl RT
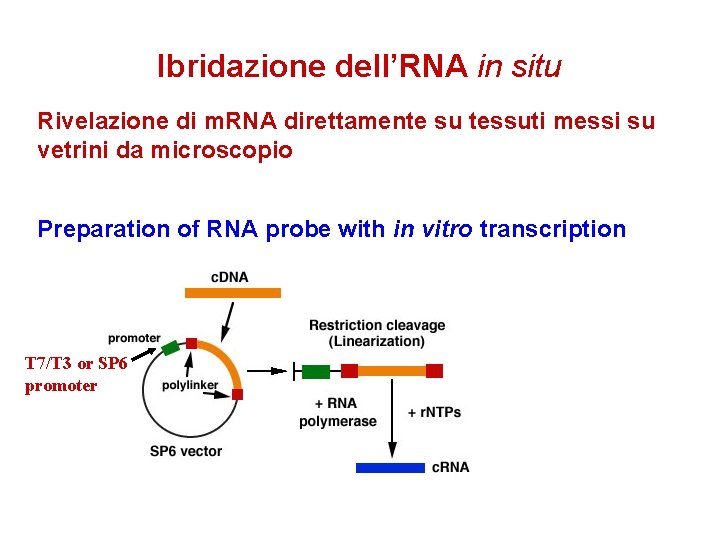
Ibridazione dell’RNA in situ Rivelazione di m. RNA direttamente su tessuti messi su vetrini da microscopio Preparation of RNA probe with in vitro transcription T 7/T 3 or SP 6 promoter
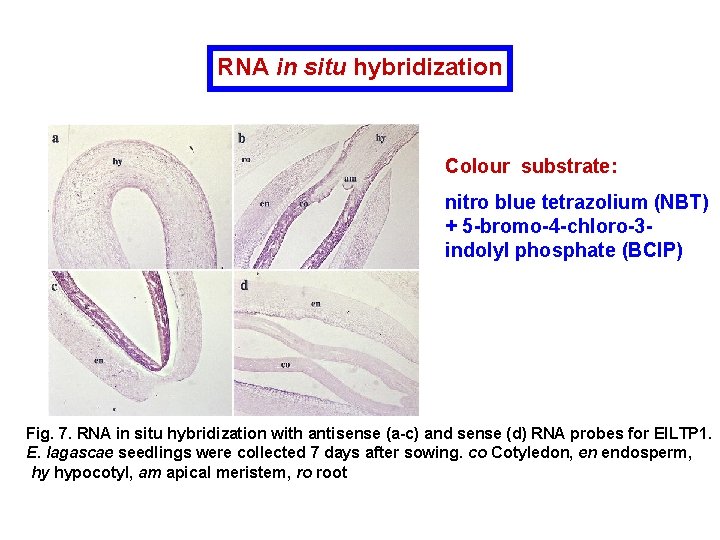
RNA in situ hybridization Colour substrate: nitro blue tetrazolium (NBT) + 5 -bromo-4 -chloro-3 indolyl phosphate (BCIP) Fig. 7. RNA in situ hybridization with antisense (a-c) and sense (d) RNA probes for El. LTP 1. E. lagascae seedlings were collected 7 days after sowing. co Cotyledon, en endosperm, hy hypocotyl, am apical meristem, ro root
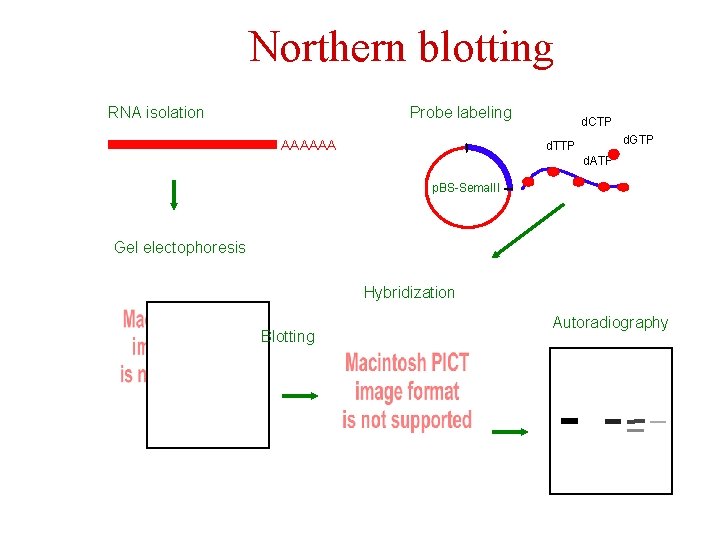
Northern blotting RNA isolation Probe labeling AAAAAA d. CTP d. GTP d. TTP d. ATP p. BS-Sema. III Gel electophoresis Hybridization Blotting Autoradiography

reverse Northern blotting Northern reverse Northern

c. DNA arrays (continued) • macro-arrays – low-density – filter-supported – radioactive probes (duplicates) – low sensitivity – only c. DNA clones spotted – cheap

c. DNA arrays (continued) • micro-arrays – high-density – glass-supported – fluorescent probes (single slide) – high sensitivity – ability to spot oligonucleotides – very expensive
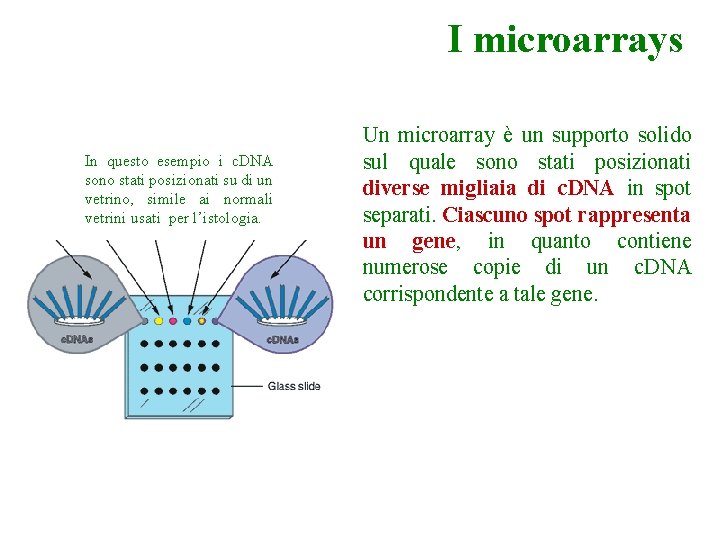
Tessuto della prostata, normale Tessuto della prostata, tumorale In questo esempio i c. DNA sono stati posizionati su di un vetrino, simile ai normali vetrini usati per l’istologia. I microarrays Un microarray è un supporto solido sul quale sono stati posizionati diverse migliaia di c. DNA in spot separati. Ciascuno spot rappresenta un gene, in quanto contiene numerose copie di un c. DNA corrispondente a tale gene.

Microarray technology Probes Microarray synthetized by photolithography or EST/oligo “linking” http: //www. ym. edu. tw/excellence/HBP_CP 4/procedure. htm
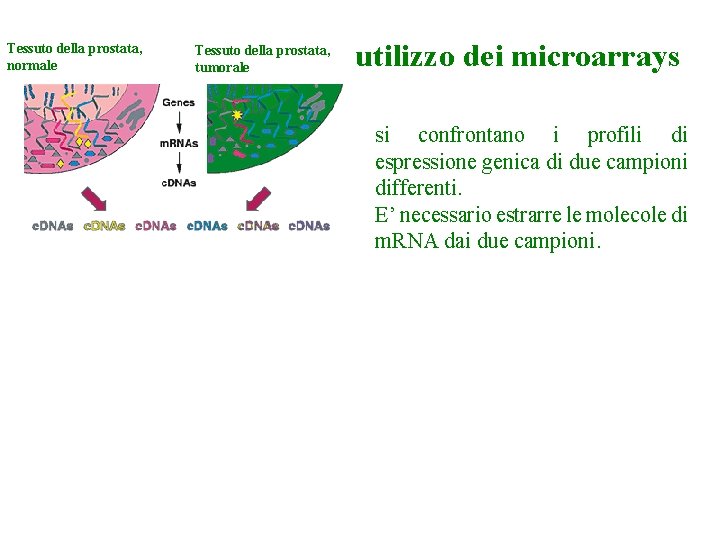
Tessuto della prostata, normale Tessuto della prostata, tumorale utilizzo dei microarrays si confrontano i profili di espressione genica di due campioni differenti. E’ necessario estrarre le molecole di m. RNA dai due campioni.
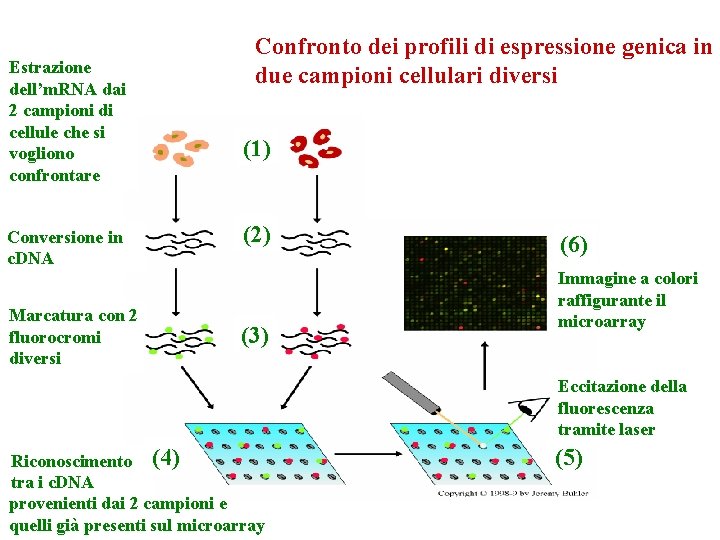
Estrazione dell’m. RNA dai 2 campioni di cellule che si vogliono confrontare Conversione in c. DNA Marcatura con 2 fluorocromi diversi Confronto dei profili di espressione genica in due campioni cellulari diversi (1) (2) (3) (6) Immagine a colori raffigurante il microarray Eccitazione della fluorescenza tramite laser Riconoscimento (4) tra i c. DNA provenienti dai 2 campioni e quelli già presenti sul microarray (5)
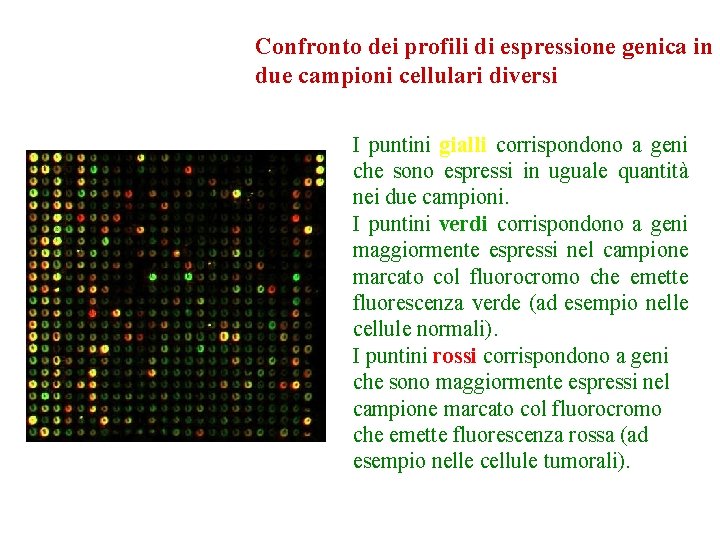
Confronto dei profili di espressione genica in due campioni cellulari diversi I puntini gialli corrispondono a geni che sono espressi in uguale quantità nei due campioni. I puntini verdi corrispondono a geni maggiormente espressi nel campione marcato col fluorocromo che emette fluorescenza verde (ad esempio nelle cellule normali). I puntini rossi corrispondono a geni che sono maggiormente espressi nel campione marcato col fluorocromo che emette fluorescenza rossa (ad esempio nelle cellule tumorali).
- Slides: 32