Metabolisme asam nukleat II Merupakan proses metabolisme informasi

Metabolisme asam nukleat II

Merupakan proses metabolisme informasi, yang berbeda dgn metabolisme-metabolisme yang telah dipelajari sebelumnya: metabolisme intermediate ensim berperanan dlm setiap reaksi yg terjadi. Ø Proses perlekatan substrat dan menghasilkan produk Ø Metabolisme informasi ada cetakan yang perlu diterjemahkan menjadi produk. Ø Cetakan DNA atau RNA, proses juga melibatkan berbagai enzim Ø
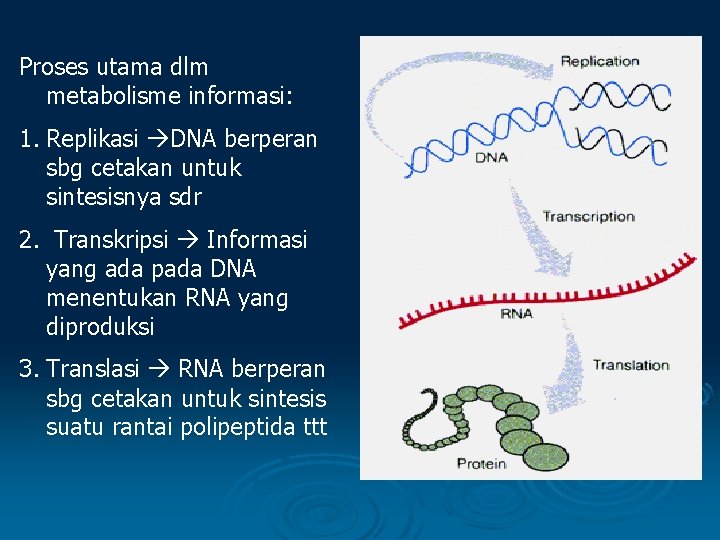
Proses utama dlm metabolisme informasi: 1. Replikasi DNA berperan sbg cetakan untuk sintesisnya sdr 2. Transkripsi Informasi yang ada pada DNA menentukan RNA yang diproduksi 3. Translasi RNA berperan sbg cetakan untuk sintesis suatu rantai polipeptida ttt

Replikasi dan transkripsi hanya menggunakan 4 nukleotida Ø Translasi mengubah bahasa nukleotida yg terdiri dari 4 nukleotida menjadi bahasa protein yang terdiri dari 20 huruf asam amino Ø Persamaan replikasi, transkripsi dan translasi membutuhkan cetakan proses terdiri dari inisiasi, elongasi dan terminasi Ø
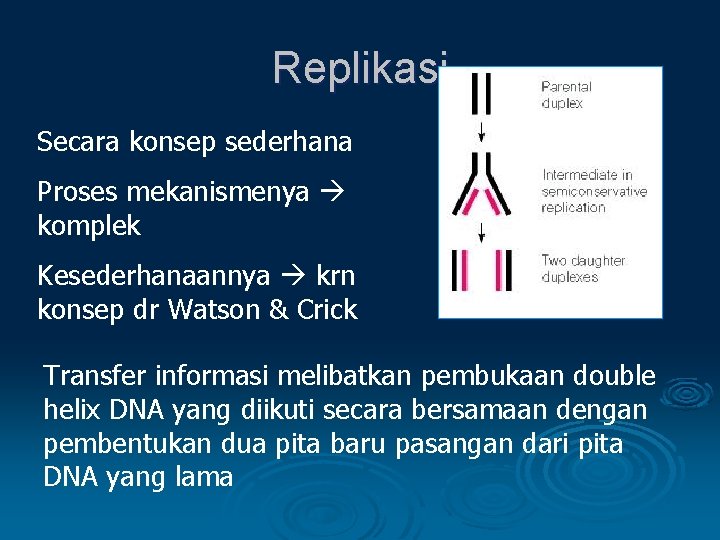
Replikasi Secara konsep sederhana Proses mekanismenya komplek Kesederhanaannya krn konsep dr Watson & Crick Transfer informasi melibatkan pembukaan double helix DNA yang diikuti secara bersamaan dengan pembentukan dua pita baru pasangan dari pita DNA yang lama
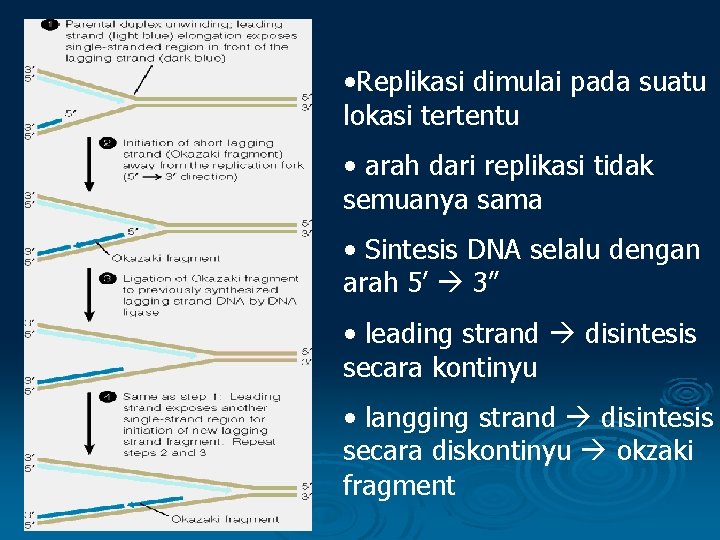
• Replikasi dimulai pada suatu lokasi tertentu • arah dari replikasi tidak semuanya sama • Sintesis DNA selalu dengan arah 5’ 3” • leading strand disintesis secara kontinyu • langging strand disintesis secara diskontinyu okzaki fragment

Proses inisiasi replikasi DNA Ø Urutan nukleotida yang secara spesifik terikat pada protein inisiasi Ø Mekanisme untuk mensintesi primer RNA dpt dielongasi oleh DNA polimerase Ø Inisiasi DNA replikasi pada E coli Ori C
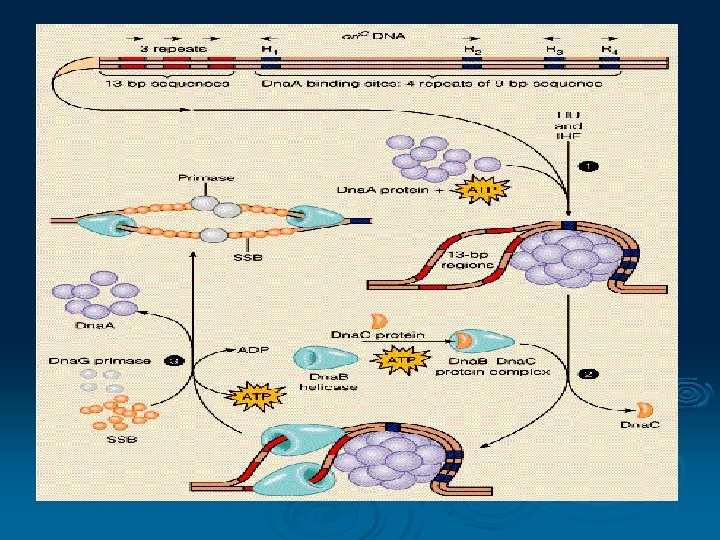
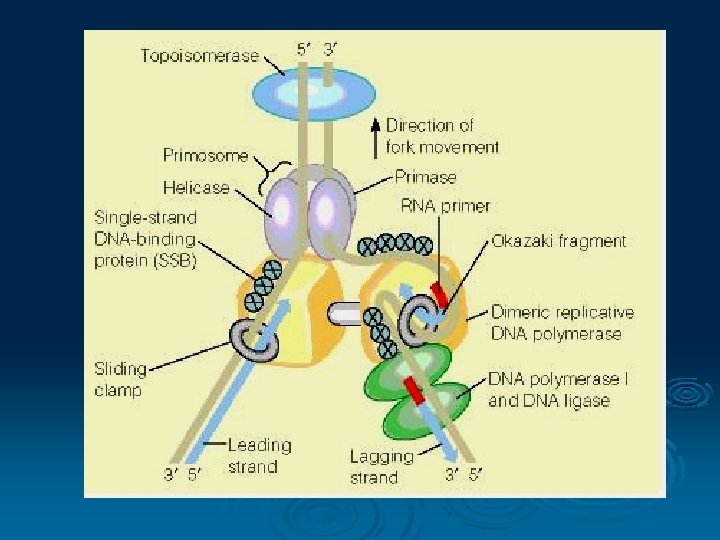
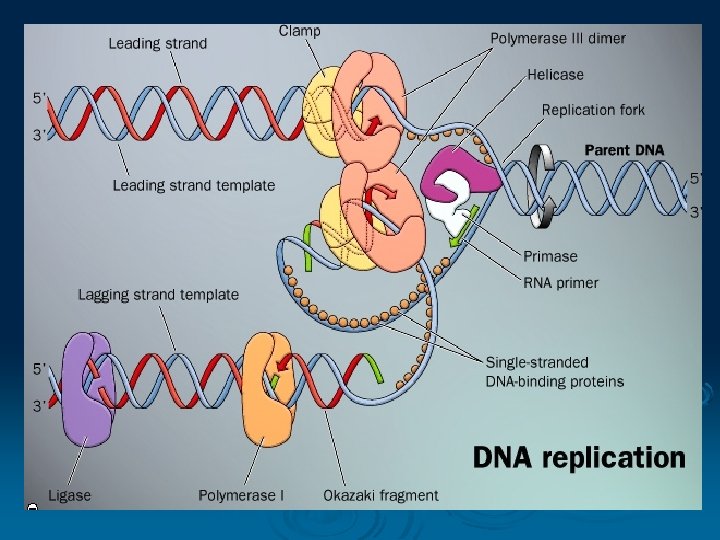

Helicase membuka double helix DNA Ø Primase mensintesis primer RNA Ø Topoisomerase melepaskan torsi krn proses membukanya DNA Ø DNA polymerase dimer, melakukan elongasi baik pd lagging dan leading strand Ø Sliding clamp memegang rantai polipeptida baru dengan cetakannya Ø Single strand DNA binding Protein SSBP menstabilkan cetakan DNA memfasilitasi pengikatan nukleotida baru Ø

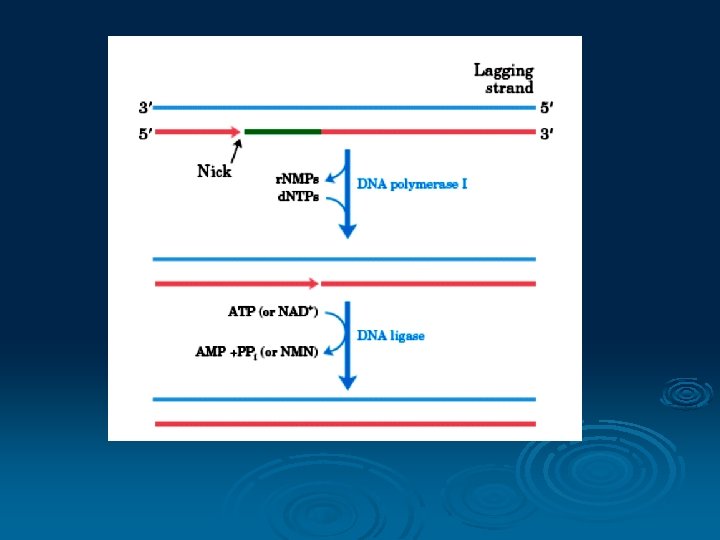
Ø DNA polimerasi I menghilangkan RNA primer yang melekat pada lagging strand DNA dan mengganti dgn DNA, Ø DNA Ligase menyambung DNA antara okazaki fragment satu dgn yg lain
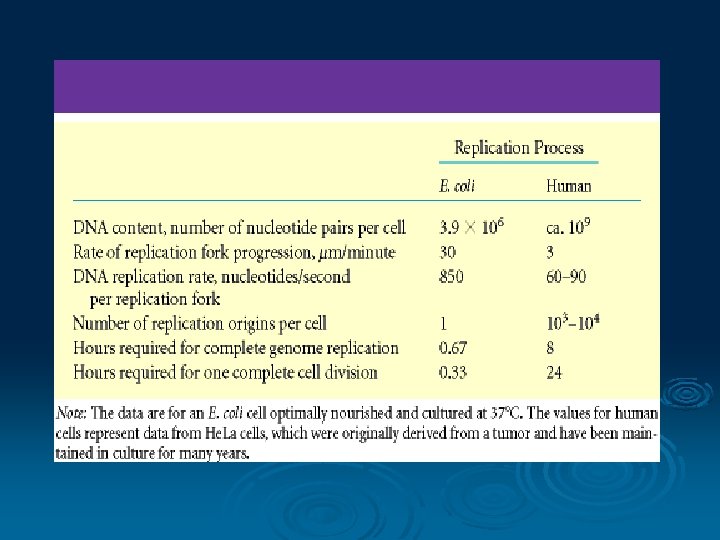
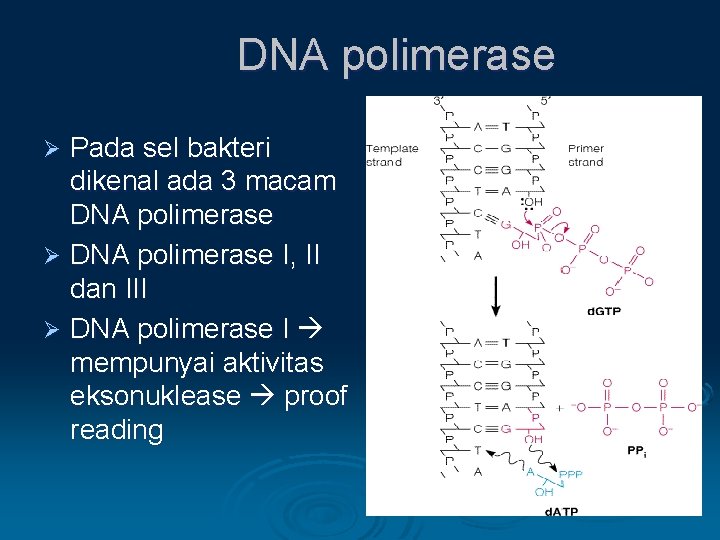
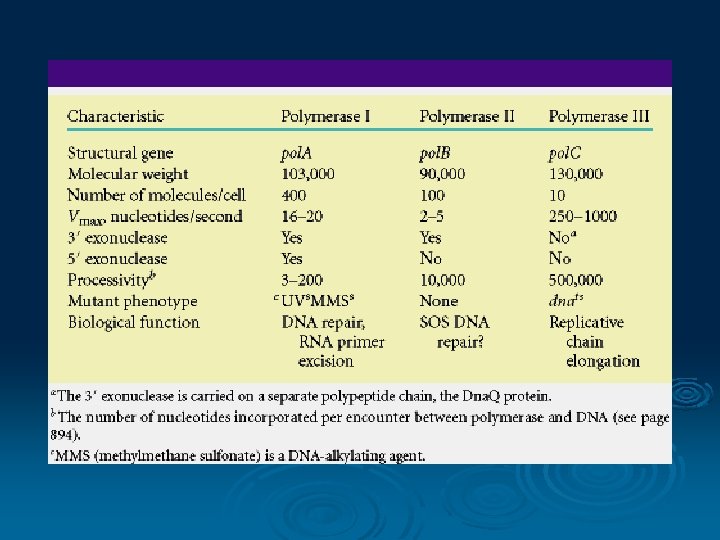
DNA polimerase Pada sel bakteri dikenal ada 3 macam DNA polimerase Ø DNA polimerase I, II dan III Ø DNA polimerase I mempunyai aktivitas eksonuklease proof reading Ø

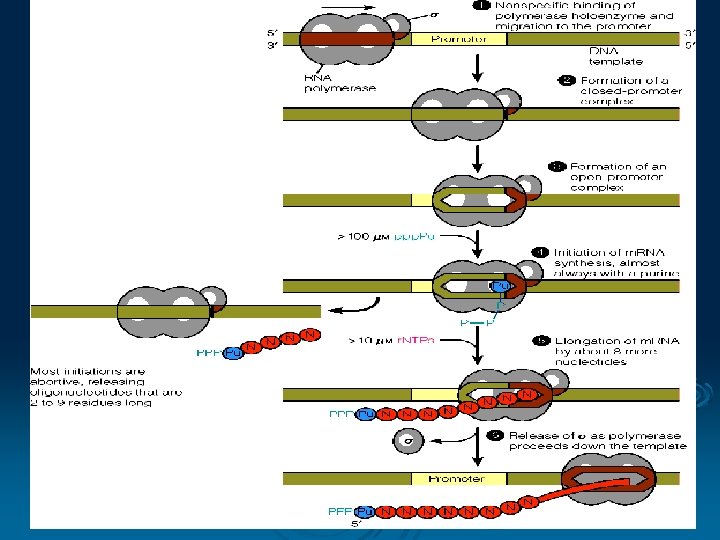
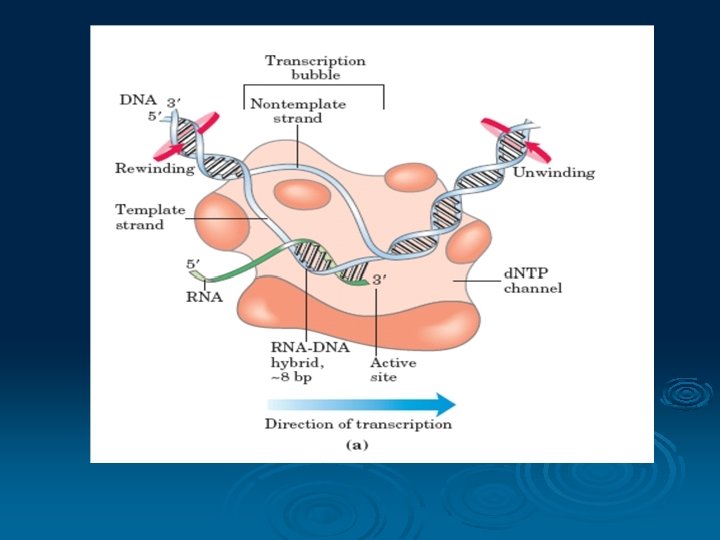
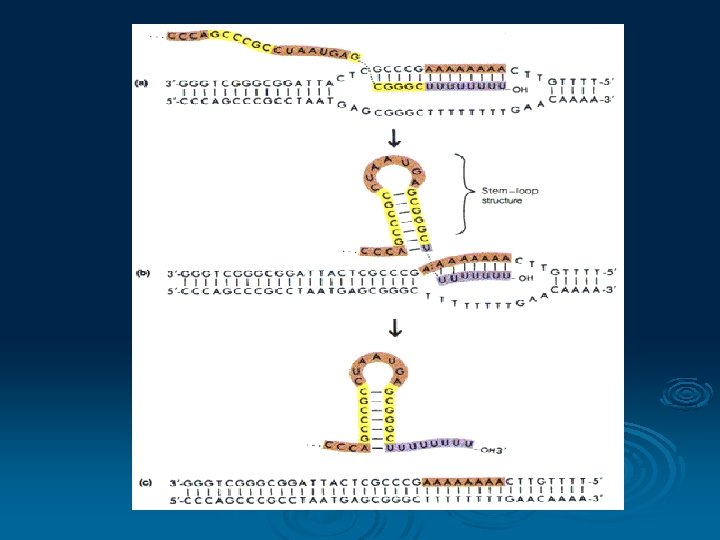
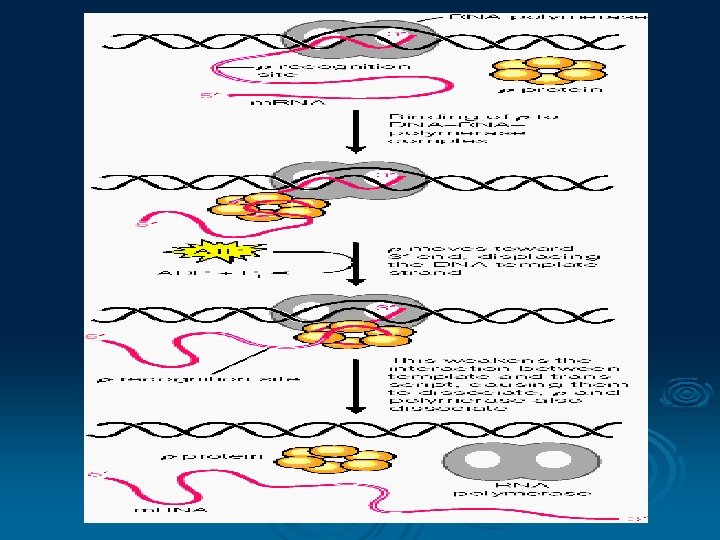
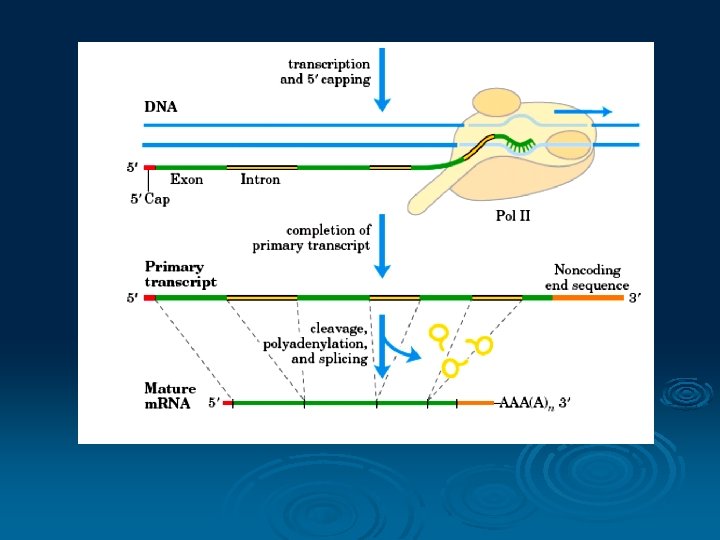
Transkripsi DNA Ø Suatu proses untuk membaca informasi yang disimpan dalam urutan nukleotida DNA RNA Ø RNA sintesis membutuhkan ensim RNA polimerase Ø Mekanisme dibagi menjadi 3 l l l Inisiasi Elongasi Terminasi

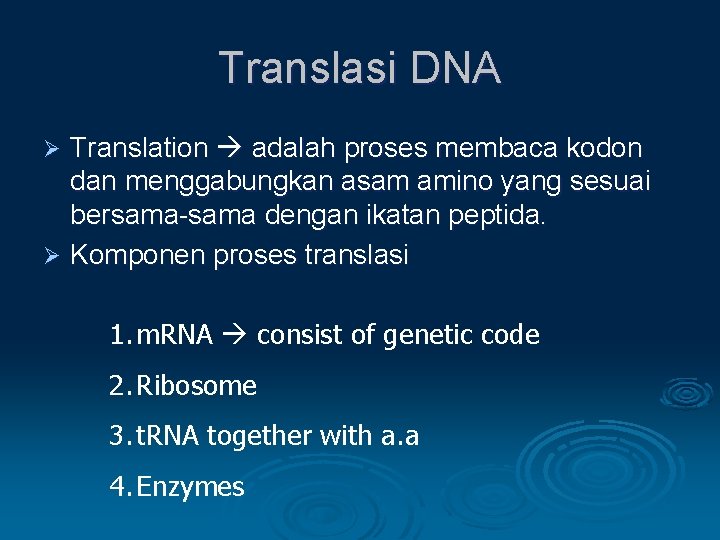
Translasi DNA Translation adalah proses membaca kodon dan menggabungkan asam amino yang sesuai bersama-sama dengan ikatan peptida. Ø Komponen proses translasi Ø 1. m. RNA consist of genetic code 2. Ribosome 3. t. RNA together with a. a 4. Enzymes

Translation process consists of 3 main stages • Initiation • Elongation • Termination Initiation Activation of amino acids for incorporation into proteins.
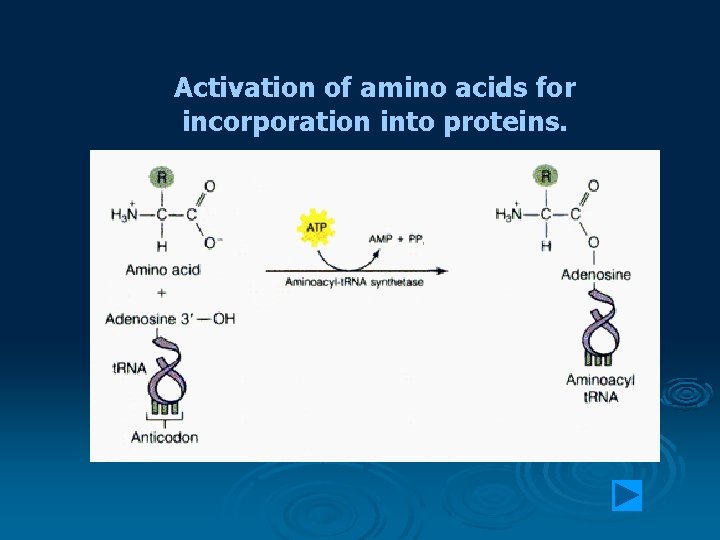
Activation of amino acids for incorporation into proteins.

Genetic code 3 nucleotides - codon – mengkode untuk 1 asam amino dlm suatu protein Codon urutan 3 nukleotida dalam m. RNA yang menspesifikasikan penggabungan suata asam amino ttt mjd protein. The relationship between codons and the amino acids they code for is called the genetic code.
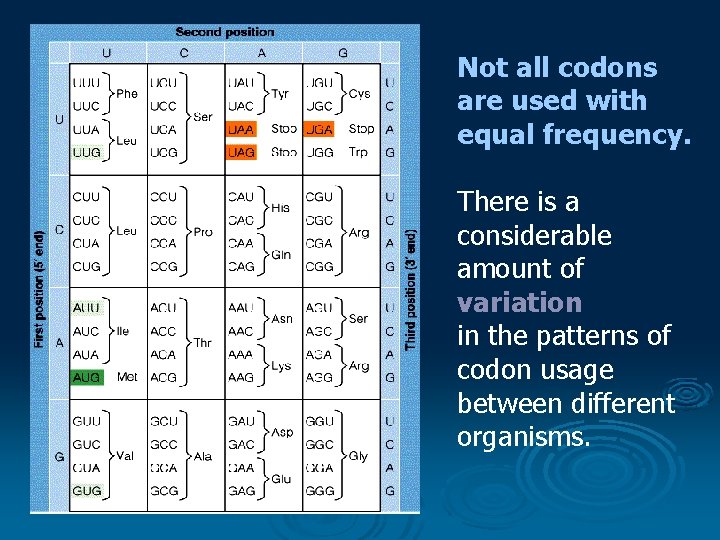
Not all codons are used with equal frequency. There is a considerable amount of variation in the patterns of codon usage between different organisms.
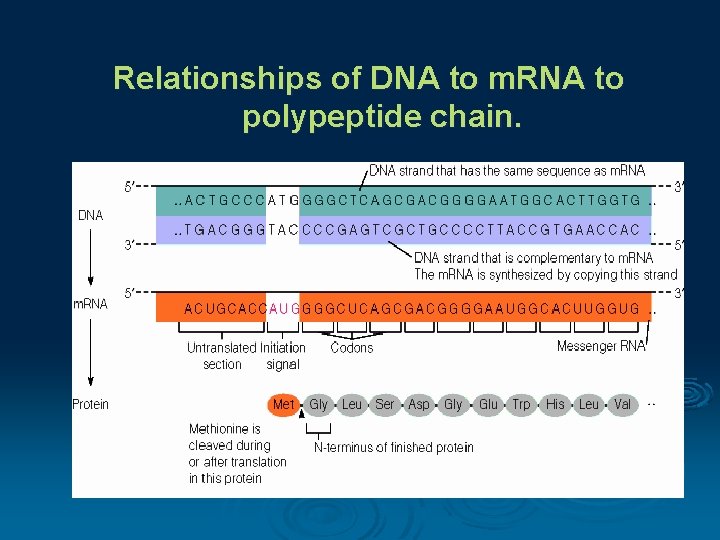
Relationships of DNA to m. RNA to polypeptide chain.
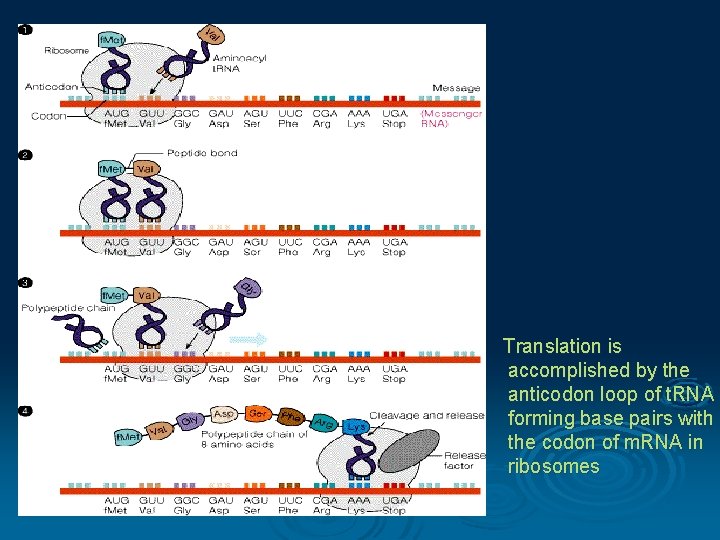
Translation is accomplished by the anticodon loop of t. RNA forming base pairs with the codon of m. RNA in ribosomes
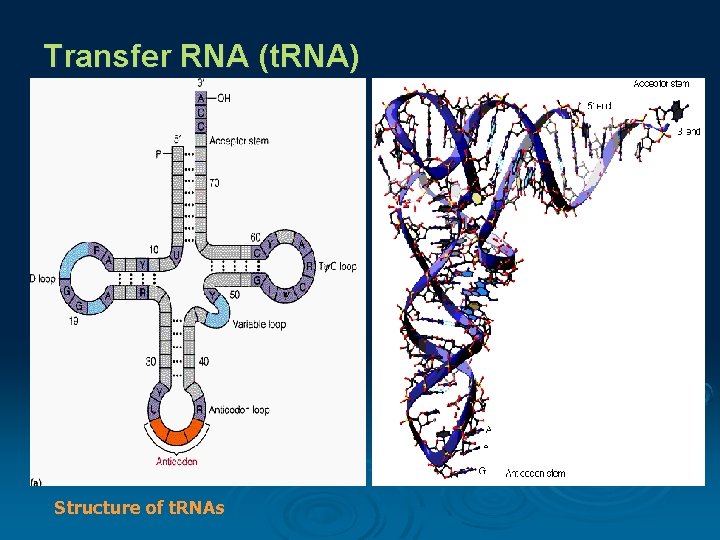
Transfer RNA (t. RNA) composed of a nucleic acid and a specific amino acid provide the link between the nucleic acid sequence of m. RNA and the amino acid sequence it codes for. An anticodon a sequence of 3 nucleotides in a t. RNA that is complementary to a codon of m. RNA Structure of t. RNAs
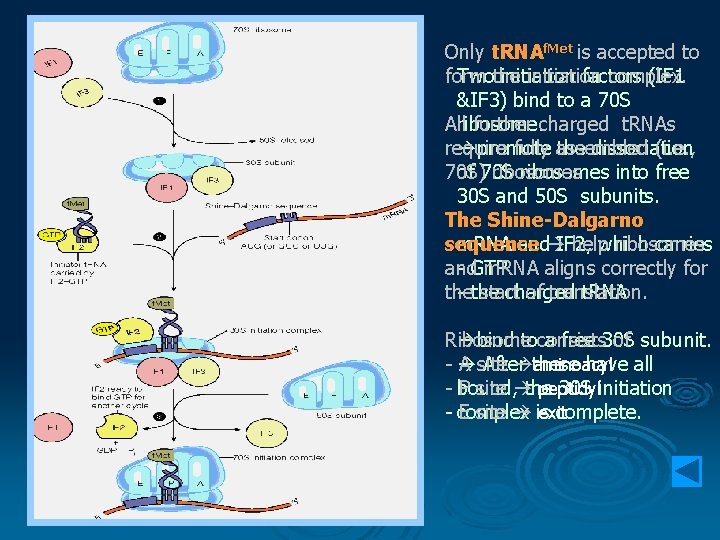
Only t. RNAf. Met is accepted to form Twothe initiation factors complex. (IF 1 &IF 3) bind to a 70 S Allribosome. further charged t. RNAs require promote fully assembled the dissociation (i. e. , 70 S) ribosomes of 70 S ribosomes into free 30 S and 50 S subunits. The Shine-Dalgarno sequence help ribosomes m. RNA and IF 2, which carries and - GTP m. RNA aligns correctly for the start of translation. - the charged t. RNA bind toconsists a free 30 S Ribosome of subunit. - A site After these aminoacyl have all - bound, P site the peptidyl 30 S initiation - complex E site is exit complete.
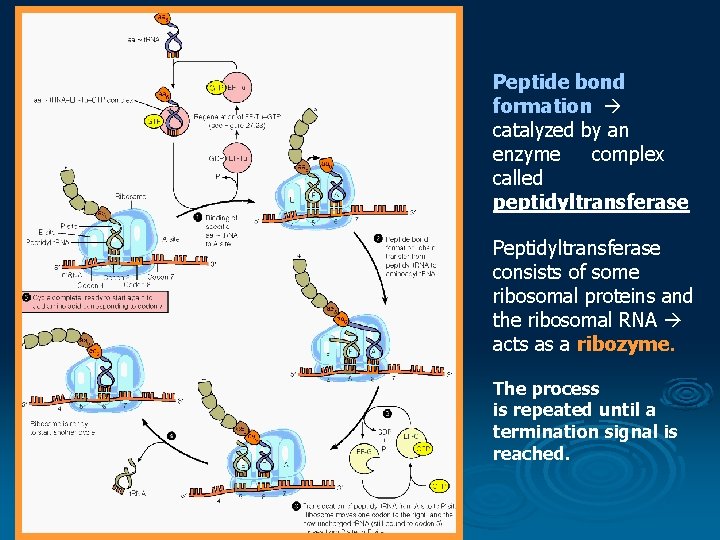
Peptide bond formation catalyzed by an enzyme complex called peptidyltransferase Peptidyltransferase consists of some ribosomal proteins and the ribosomal RNA acts as a ribozyme. The process is repeated until a termination signal is reached.
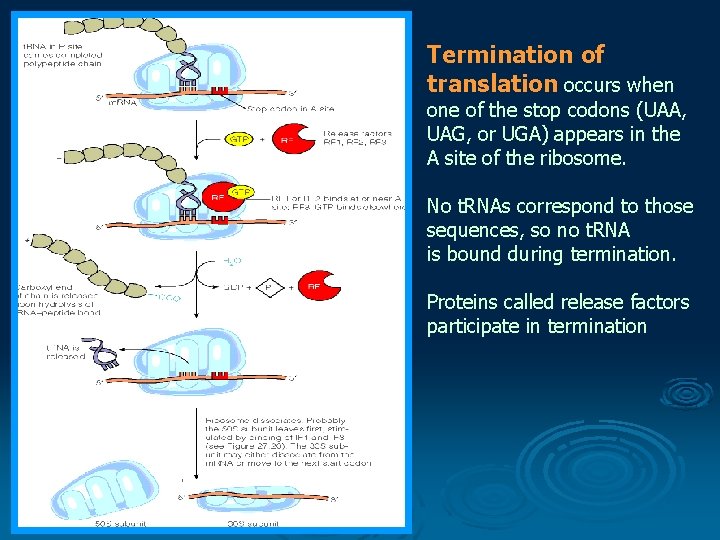
Termination of translation occurs when one of the stop codons (UAA, UAG, or UGA) appears in the A site of the ribosome. No t. RNAs correspond to those sequences, so no t. RNA is bound during termination. Proteins called release factors participate in termination


Sampai jumpa dan Good luck to ur exam
- Slides: 36