Marcatori Molecolari v Introduzione v Marcatori RAPD v






- Slides: 22

Marcatori Molecolari v Introduzione v Marcatori RAPD v Marcatori proteici v Marcatori STS v DNA v Marcatori AFLP v Marcatori RFLP v Tecniche elettroforesi v PCR v Considerazioni v Applicazioni

Introduzione v I fattori ambientali possono influenzare i caratteri morfologici v I marcatori molecolari (MM) focalizzano la diversità del materiale genetico e misurano le variazioni controllate da geni v. I MM possono essere usati per : ümisurare diversità genetica ü costituire mappe genetiche ü selezione assistita (MAS) ü supporto all’isolamento genico (PC) Che cosa sono i Marcatori Molecolari ? ? v Marcatori Molecolari üsequenze proteiche e di DNA facilmente individuabili e la cui eredità può essere controllata v Polimorfismo in proteine üproteine del seme üisoenzimi ed alloenzimi v. Polimorfismi di DNA ünucleare ücitoplasmatico

Proprietà desiderabili v Polimorfico v Eredità codominante v Distribuito in tutto il genoma v Facile e veloce da individuare v Poco costoso v Riproducibile / Trasferibile v Nessun marcatore le possiede tutte Marcatori proteici v Breve introduzione alle proteine v Proteine di conservazione del seme v Isoenzimi v Alloenzimi

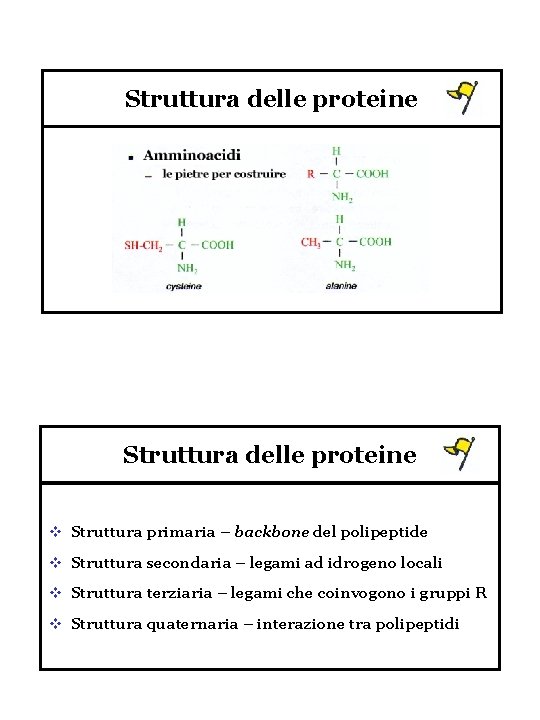
Struttura delle proteine v Struttura primaria – backbone del polipeptide v Struttura secondaria – legami ad idrogeno locali v Struttura terziaria – legami che coinvogono i gruppi R v Struttura quaternaria – interazione tra polipeptidi

Proteine ed ambiente v La struttura tridimensionale delle proteine è il risultato dell’interazione con l’ambiente. v Bisogna quindi tenere conto della denaturazione delle proteine …. v …. e della diversità della loro funzione … ü…facilitata dalla complessità di struttura Proteine seed storage § Perché usiamo le proteine del seme ? ? • • • § i semi sono ricchi di proteine le proteine sono disponibili in sufficiente quantità i semi sono uno stadio dello sviluppo ben definito La metodologia • • • si estraggono le proteine e si separano in elettroforesi si visualizzano sul gel con la colorazione (staining) si analizza il pattern delle bande

Considerazioni ed Applicazioni § Considerazioni • • • § co-migrazione pattern delle bande complesso variazione intraspecifica Applicazione della tecnica • • es. frumento, orzo recentemente anche melanzana Isoenzimi ed Alloenzimi § Forme multiple dello stesso enzima • isoenzima : un enzima, più di un locus genico • alloenzima : un enzima, un locus genico § Metodologie • tessuti macerati • enzimi separati per elettroforesi • visualizzazione per colorazione istochimica • analisi del pattern

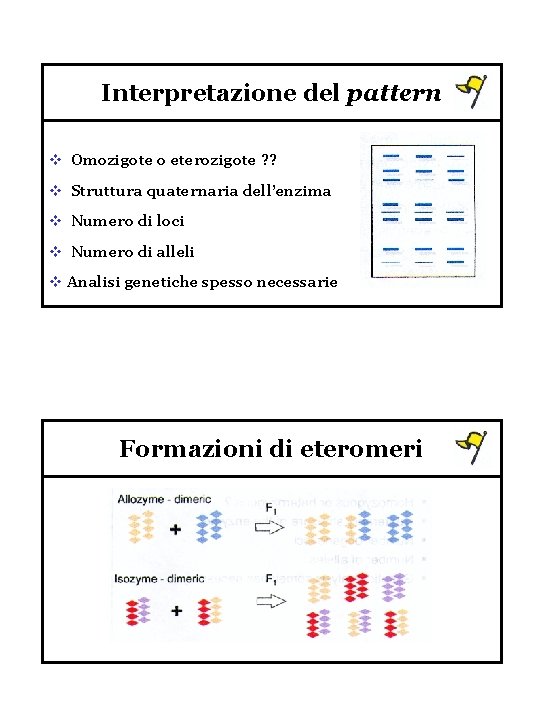
Interpretazione del pattern v Omozigote o eterozigote ? ? v Struttura quaternaria dell’enzima v Numero di loci v Numero di alleli v Analisi genetiche spesso necessarie Formazioni di eteromeri

Applicazioni § Metodo potente e riproducibile per : • • • § caratterizzare/identificare genotipi studi di genetica di popolazione esaminare patterns di variazione geografica Limitato numero di enzimi disponibili Marcatori su DNA v Le basi del DNA v Metodo RFLP v Metodi basati sulla PCR v Marcatori STS v Marcatori AFLP v Tecniche elettroforesi

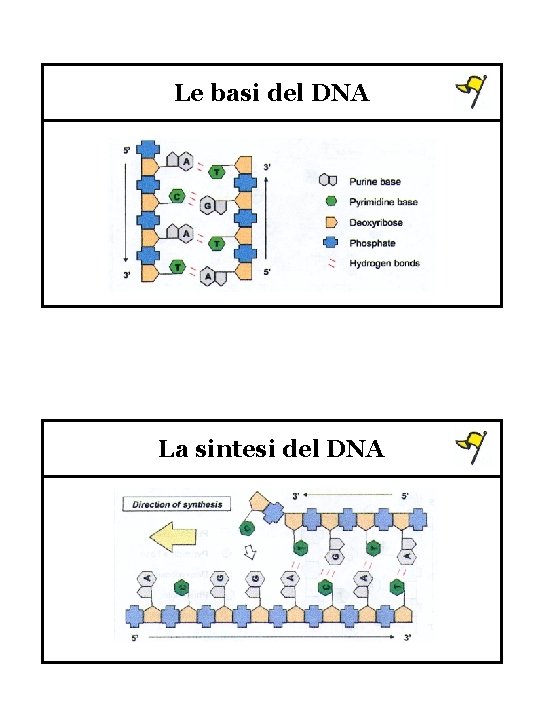
Le basi del DNA La sintesi del DNA

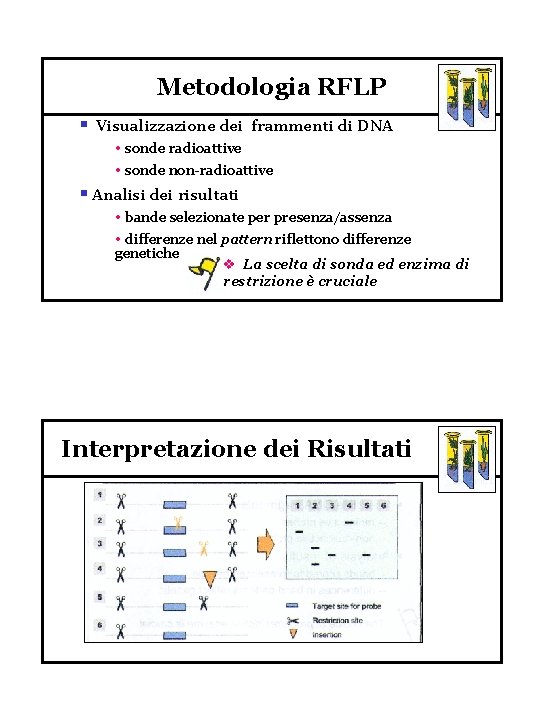
Marcatori RFLP Restriction Fragment Length Polymorphism § Gli RFLP esaminano differenze in peso molecolare di specifici frammenti di DNA ristretti § Usualmente si utilizza il DNA totale § Richiedono DNA puro e di alto peso molecolare Metodologia RFLP § Tagliare il DNA in piccoli frammenti § Separare i frammenti in gel eletttroforesi § Trasferire i frammenti di DNA su filtro

Metodologia RFLP § Visualizzazione dei frammenti di DNA • sonde radioattive • sonde non-radioattive § Analisi dei risultati • bande selezionate per presenza/assenza • differenze nel pattern riflettono differenze genetiche v La scelta di sonda ed enzima di restrizione è cruciale Interpretazione dei Risultati

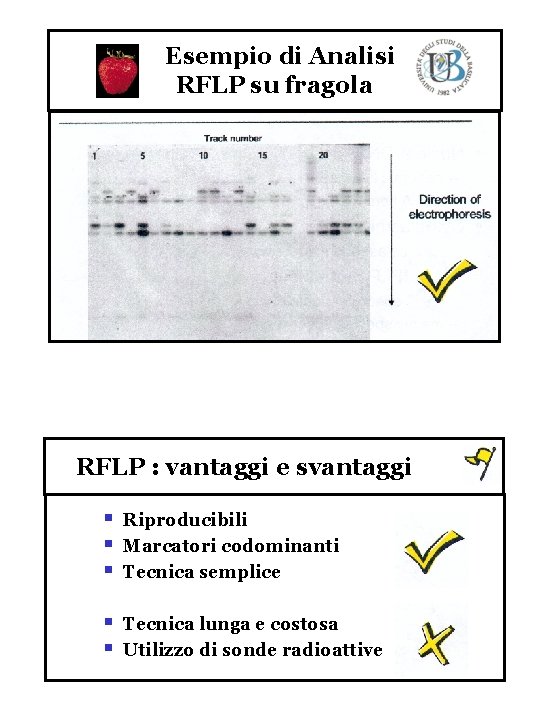
Esempio di Analisi RFLP su fragola RFLP : vantaggi e svantaggi § § § Riproducibili Marcatori codominanti Tecnica semplice § § Tecnica lunga e costosa Utilizzo di sonde radioattive

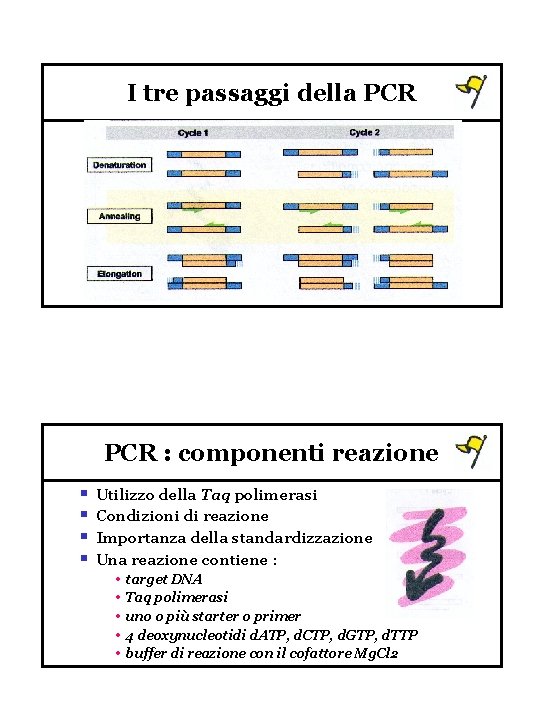
Marcatori su DNA v Le basi del DNA v Metodo RFLP v Metodi basati sulla PCR v Marcatori STS v Marcatori AFLP v Tecniche elettroforesi PCR Polymerase Chain Reaction § § Potente tecnica per amplificare il DNA Prevede l’utilizzo di cicli di temeperature • step di denaturazione • step di annealing • step di elongazione § Il DNA amplificato viene separato su gel elettroforesi

I tre passaggi della PCR : componenti reazione § § Utilizzo della Taq polimerasi Condizioni di reazione Importanza della standardizzazione Una reazione contiene : • target DNA • Taq polimerasi • uno o più starter o primer • 4 deoxynucleotidi d. ATP, d. CTP, d. GTP, d. TTP • buffer di reazione con il cofattore Mg. Cl 2

PCR : riassunto § DNA polimerasi § Apparecchio Thermal Cycler § Profilo delle temperatura (programma) § Concentrazione del DNA target § Concentrazione dello ione Mg RAPD Random Amplified Polymorphic DNA § Tratti di DNA anonimi amplificati utilizzando primer arbitrari § Metodo veloce per individuare polimorfismi § Marcatori dominanti § Problemi di riproducibilità

Interpretazione dei RAPDs § I marcatori RAPDs sono anonimi § I marcatori RAPDs sono dominanti § Problemi di co-migrazione Øuna banda, un frammento ? Ø stessa banda, stesso frammento ? RFLP : vantaggi e svantaggi § § § Semplici e veloci Poco costosi Non utilizza radioattivo § § § Marcatori dominanti Problemi di riproducibilità Problemi di interpretazione

Marcatori su DNA v Le basi del DNA v Metodo RFLP v Metodi basati sulla PCR v Marcatori STS v Marcatori AFLP v Tecniche elettroforesi STS Sequence-Tagged Sites § Utilizzano la PCR a partire da : Ø Sequence-Tagged Microsatellites (STMS) Ø Oligonucleotidi ancorati a MS ü inter-simple sequence repeat (ISSR) Ø Sequence-characterized amplified regions (SCARs) Ø Cleaved amplified polymorphic sequence (CAPS)

Marcatori Microsatelliti § Sequence-Tagged MS § ü Codominante Inter-simple sequence repeats ü In genere single locus multiallelico ü Amplificano segmenti adiacenti sequenze ripetute (repeats) ü Marcatori dominanti SCARs and CAPS § SCARs – sequence characterized amplified regions Ømarcatore single locus derivante da frammento RAPD § CAPS – cleaved amplified polymorphic sequence ØMarcatore locus specifico ØProdotto di amplificazione RAPD utilizzato come sonda RFLP

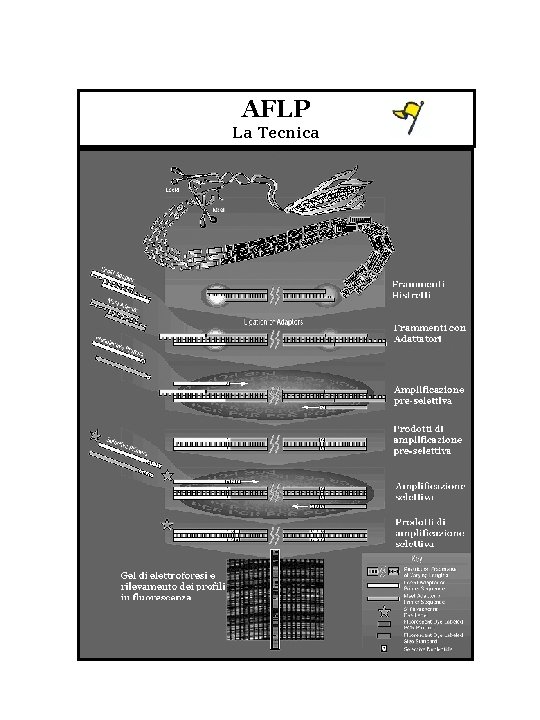
Marcatori su DNA v Le basi del DNA v Metodo RFLP v Metodi basati sulla PCR v Marcatori STS v Marcatori AFLP v Tecniche elettroforesi AFLP Amplified Fragment Length Polymorphism § Tecnicamente sfruttano la combinazione tra RFLP e PCR § Il risultato è un fingerprint altamente informativo § Il metodo diviene sempre più popolare

AFLP La Tecnica

AFLP : vantaggi e svantaggi § § § Altamente sensibili Altamente riproducibili Largamente applicabili § Costosi § Tecnicamente difficili § Necessari radioisotopi § Problemi di interpretazione Analisi RAPD su melanzana

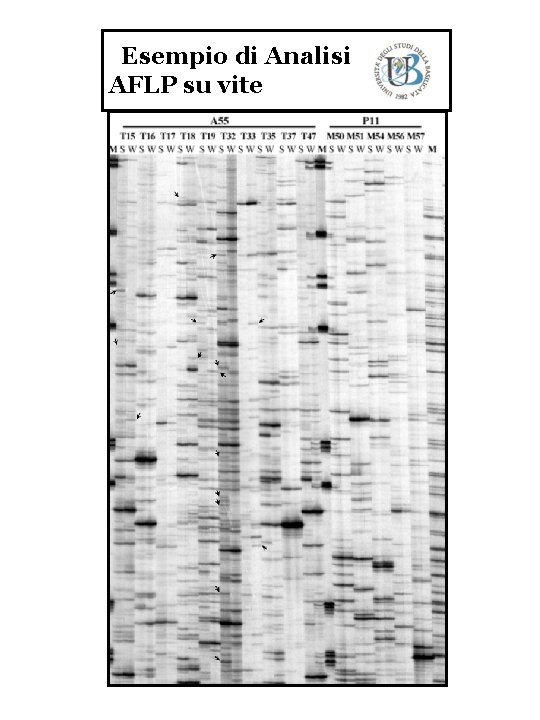
Esempio di Analisi AFLP su vite