Les subtlomres des chromosomes des hmiascomyctes Ccile Fairhead

Les subtélomères des chromosomes des hémiascomycètes Cécile Fairhead Génétique Moléculaire des Levures Institut Pasteur, Paris. Nantes, 12 -13 octobre 2006
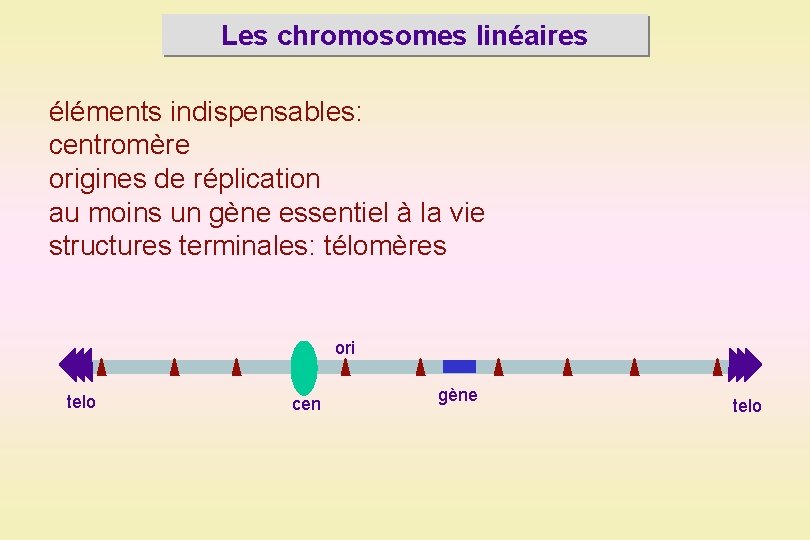
Les chromosomes linéaires éléments indispensables: centromère origines de réplication au moins un gène essentiel à la vie structures terminales: télomères ori telo cen gène telo
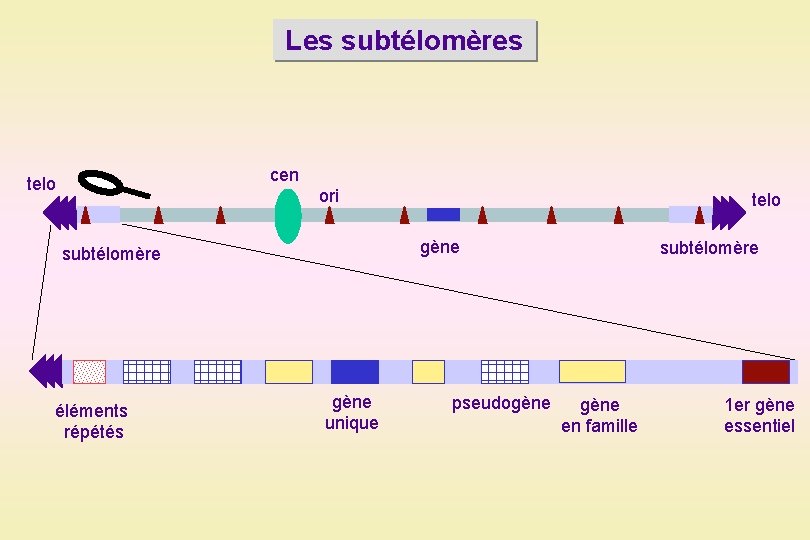
Les subtélomères cen telo ori gène subtélomère éléments répétés telo gène unique pseudogène subtélomère gène en famille 1 er gène essentiel
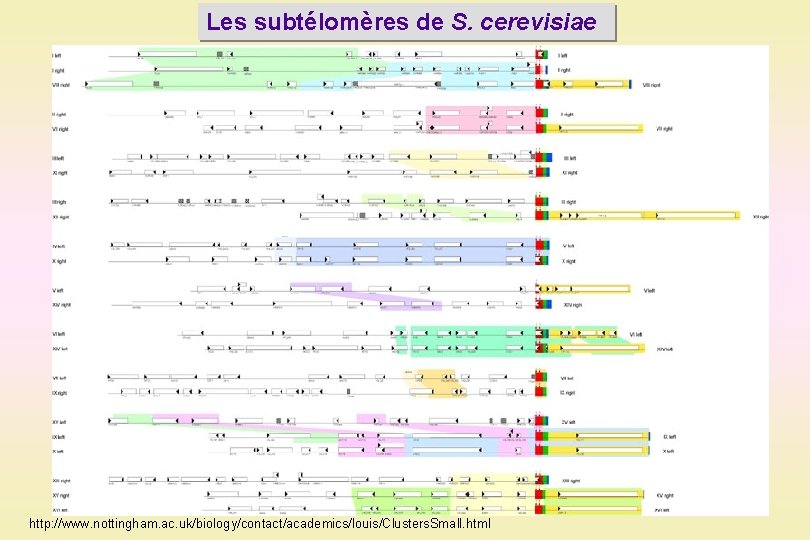
Les subtélomères de S. cerevisiae http: //www. nottingham. ac. uk/biology/contact/academics/louis/Clusters. Small. html

Les gènes dans les subtélomères Homo sapiens: grandes familles de gènes de récepteurs olfactifs Parasites (malaria et autres): familles de gènes d'antigènes de surface, gènes mobiles ou expression différentielle (échappement au système immunitaire) Champignons filamenteux phytopathogènes: familles de gènes de protéines de surface (virulence) Levures : "alimentaires": familles de gènes de flocculines, et d'utilisation des sucres du milieu "pathogènes": familles de gènes d'adhésion aux epitheliums
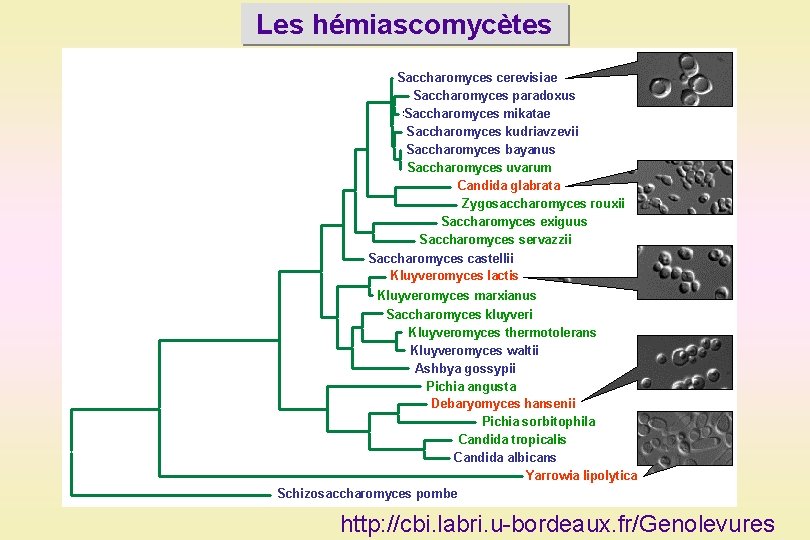
Les hémiascomycètes http: //cbi. labri. u-bordeaux. fr/Genolevures

Subtelomeric gene families in S. cerevisiae and their putative homologs I In Saccharomyces species

Subtelomeric gene families in S. cerevisiae and their putative homologs II In other species

Le gène FLO 1 de S. cerevisiae DNA self-matrix Repeats (minisatellites) generate diversity in these proteins involved in cell-cell adhesion

Subtélomères de K. lactis Family of KLLA 0 A 00110 g, 7 subtelomeric members KLLA specific, unknown EL TEL KLLA 0 A 00110 g g g 10 g 0132 1 154 0 0 0 towards centromere 0 E A L L L KL KL KL 10 kb 20 kb Family of KLLA 0 A 00132 g, 7 subtelomeric members, 3 central, similar to unknown SACE subtelomeric gene KLLA 0 A 00132 g KLLA 0 A 00154 g AL towards centromere Family of KLLA 0 A 00154 g, 7 subtelomeric members KLLA specific, unknown
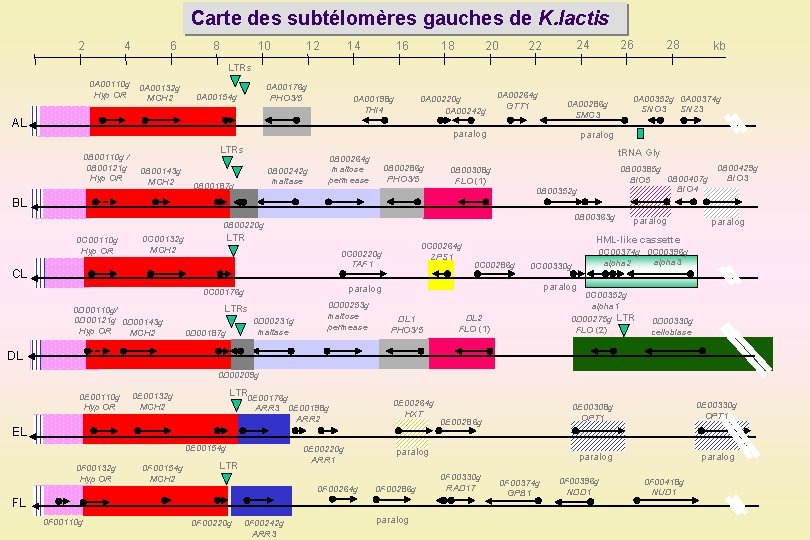
Carte des subtélomères gauches de K. lactis 2 4 6 8 10 14 12 16 18 24 22 20 28 26 kb LTRs 0 A 00110 g Hyp OR 0 A 00132 g MCH 2 0 A 00176 g PHO 3/5 0 A 00154 g 0 A 00220 g 0 A 00242 g 0 A 00198 g THI 4 AL 0 A 00264 g GTT 1 paralog 0 B 00110 g / 0 B 00121 g Hyp OR LTRs 0 B 00143 g MCH 2 0 B 00187 g paralog t. RNA Gly 0 B 00264 g maltose permease 0 B 00242 g maltase 0 A 00352 g 0 A 00374 g SNO 3 SNZ 3 0 A 00286 g SMC 3 0 B 00286 g PHO 3/5 0 B 00385 g 0 B 00407 g BIO 5 BIO 4 0 B 00308 g FLO (1) 0 B 00352 g 0 B 00429 g BIO 3 BL 0 B 00363 g 0 B 00220 g 0 C 00110 g Hyp OR LTR 0 C 00132 g MCH 2 0 C 00220 g TAF 1 CL LTRs 0 D 00231 g maltase 0 D 00187 g 0 D 00253 g maltose permease 0 C 00286 g 0 C 00374 g 0 C 00396 g alpha 3 alpha 2 0 C 00330 g paralog DL 1 PHO 3/5 paralog HML-like cassette paralog 0 C 00176 g 0 D 00110 g/ 0 D 00121 g 0 D 00143 g Hyp OR MCH 2 0 C 00264 g ZPS 1 paralog 0 C 00352 g alpha 1 0 D 00275 g LTR FLO (2) DL 2 FLO (1) 0 D 00330 g cellobiase DL 0 D 00209 g 0 E 00110 g Hyp OR LTR 0 E 00176 g 0 E 00132 g MCH 2 ARR 3 0 E 00198 g ARR 2 0 E 00264 g HXT EL 0 E 00154 g 0 F 00132 g Hyp OR 0 F 00154 g MCH 2 0 E 00220 g ARR 1 LTR 0 F 00264 g paralog 0 F 00286 g FL 0 F 00110 g 0 F 00220 g 0 F 00242 g ARR 3 0 E 00286 g paralog 0 F 00330 g RAD 17 0 F 00374 g GPB 1 0 E 00308 g OPT 1 0 E 00330 g OPT 1 paralog 0 F 00396 g NDD 1 0 F 00418 g NUD 1
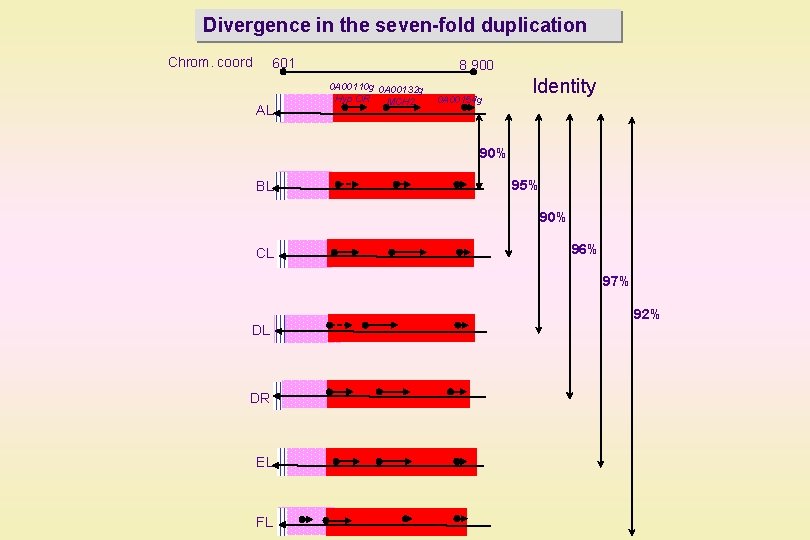
Divergence in the seven-fold duplication Chrom. coord 601 AL 8 900 0 A 00110 g 0 A 00132 g Hyp OR MCH 2 0 A 00154 g Identity 90% BL 95% 90% CL 96% 97% 92% DL DR EL FL

Protein-coding genes in subtelomeres of K. lactis. Out of 138 genes: Uniqueness In duplications Paralogs (diverged) Unique 63 (46%) 27 (19%) 48 (35%) Overall, in the genome, 68% of genes are unique Predicted or known localisation of product Unknown Extracellular, plasma membrane and cell wall Other 59 (43%) 44 (32%) 35 (25%) Overall, in the genome of S. cerevisiae, 12% of genes are known or predicted to be “external”

Subtélomères de D. hansenii 3 L subtelomeric family Tel unknown function 6 L subtelomeric family protein kinase Tel
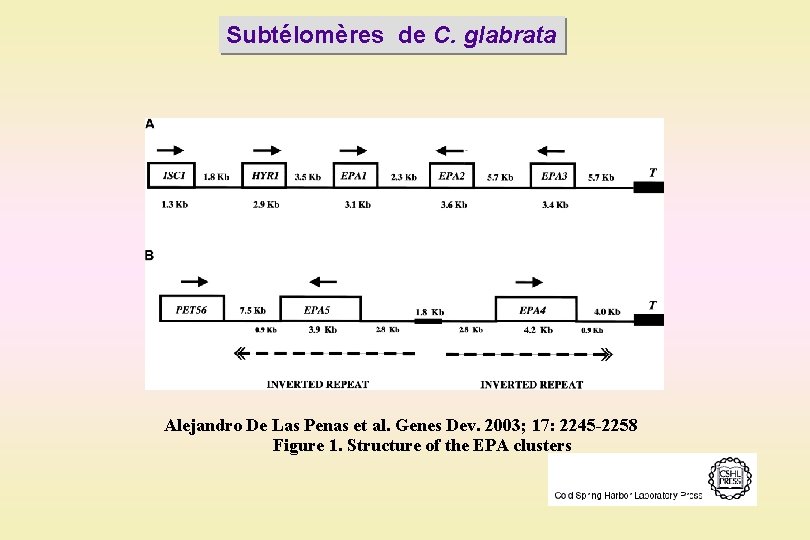
Subtélomères de C. glabrata Alejandro De Las Penas et al. Genes Dev. 2003; 17: 2245 -2258 Figure 1. Structure of the EPA clusters
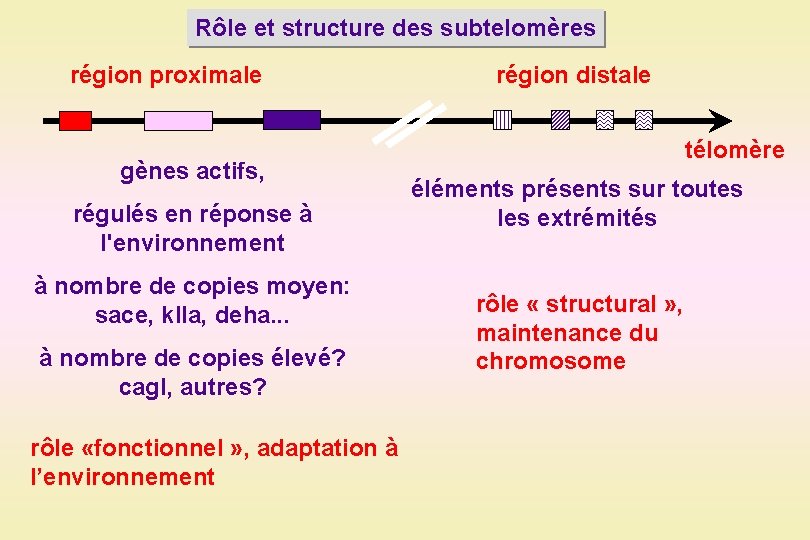
Rôle et structure des subtelomères région proximale gènes actifs, régulés en réponse à l'environnement à nombre de copies moyen: sace, klla, deha. . . à nombre de copies élevé? cagl, autres? rôle «fonctionnel » , adaptation à l’environnement région distale télomère éléments présents sur toutes les extrémités rôle « structural » , maintenance du chromosome

Rôle et structure des subtélomères -permettent la plasticité nécessaire à l’adaptation à l’environnement: contiennent des familles de gènes qui peuvent muter facilement: gènes « de contingence » = séquences homéologues qui recombinent entre elles -rôle de "back-up" en cas de perte de télomère (cassure à l’extrémité d’un chromosome, absence de télomérase) -contribuent à la divergence chromosomique entre individus et entre espèces au cours de l’évolution

Rôle et structure des subtélomères questions et directions futures: Combien de types de structures de subtélomères existe-t-il chez les hémiascomycètes? Peut-on relier le type de structure au statut sexuel de l'espèce? A sa pathogénicité? Quels sont les fonctions des gènes situés dans les subtélomères? Gènes à répétitions internes, de type "FLO": classification des types de répétitions et lien avec la fonction des protéines codées et mécanismes d'évolution de ces gènes
- Slides: 18