Leccin 7 Ligamiento y recombinacin GENES CON LOCI

Lección 7 Ligamiento y recombinación

GENES CON LOCI EN EL MISMO CROMOSOMA (GENES LIGADOS)

SEGREGACIÓN INESPERADA A principios del siglo 20 Bateson y Punnet encontraron desviaciones significativas de la segregación 9: 3: 3: 1, para ciertos caracteres en el guisante de olor P PPLL x ppll Color de las flores: Forma del polen: P (púrpura) > p (rojo) L (alargado) > l (redondo) Exceso de fenotipos doble dom y doble rec Pp. Ll [PL] [Pl] [p. L] [pl] Total Observado 284 21 21 55 381 Esperado (9: 3: 3: 1) 215 71 71 24 381

MÁS EJEMPLOS Para comprender el fenómeno es mejor utilizar cruzamientos más simples. Morgan utilizo cruzamientos prueba en Drosophila P pr+pr+vg+vg+ x prprvgvg F 1 Color de ojos: pr+ (rojo) > pr (púrpura) Desarrollo de alas: vg+ (normales) > vg (vestigiales) ♀ pr+prvg+vg X ♂ prprvgvg [pr+vg+] = 1339 [prvg] = 1195 ¿Algún problema con estos fenotipos? [pr+vg] = 151 [prvg+] = 154 ≠ ¼ ¼

MÁS EJEMPLOS En otro cruzamiento con los mismos caracteres: P pr+pr+vgvg x prprvg+vg+ F 1 ♀ pr+prvg+vg X ♂ prprvgvg [pr+vg+] = 157 [prvg] = 146 No había problemas con estos fenotipos [pr+vg] = 965 [prvg+] = 1067 ≠ ¼ ¼
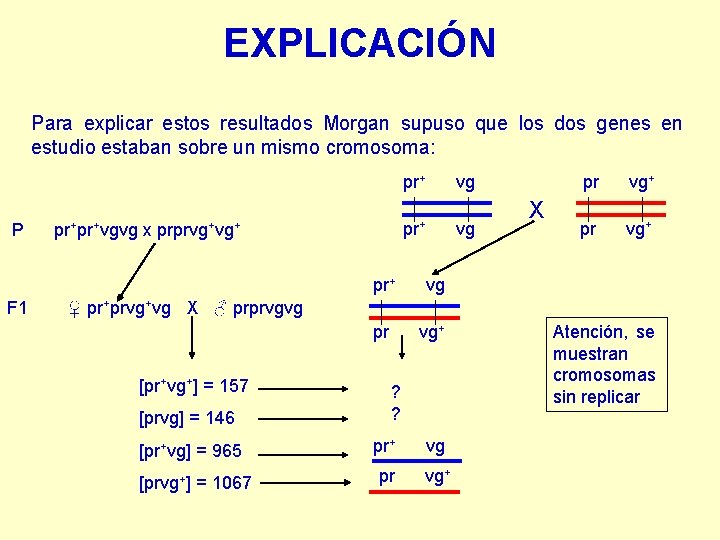
EXPLICACIÓN Para explicar estos resultados Morgan supuso que los dos genes en estudio estaban sobre un mismo cromosoma: pr+ P F 1 pr+pr+vgvg x vg pr+ prprvg+vg+ vg pr vg+ X pr vg+ ♀ pr+prvg+vg X ♂ prprvgvg [pr+vg+] = 157 [prvg] = 146 ? ? [pr+vg] = 965 pr+ vg [prvg+] = 1067 pr vg+ Atención, se muestran cromosomas sin replicar
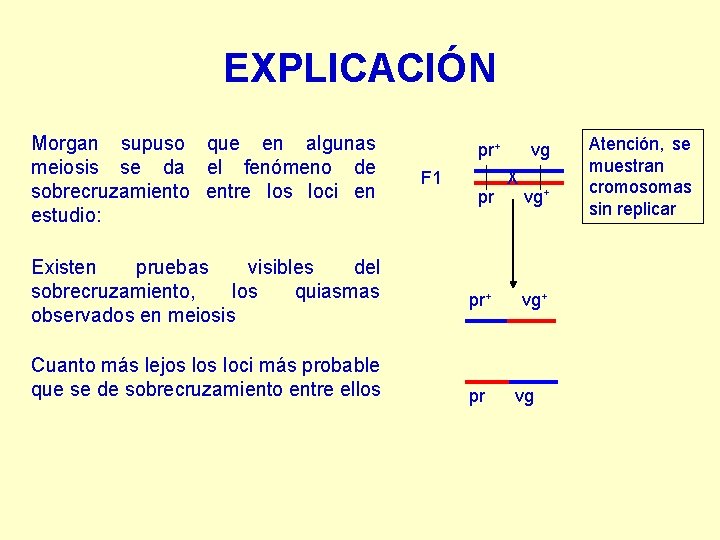
EXPLICACIÓN Morgan supuso que en algunas meiosis se da el fenómeno de sobrecruzamiento entre los loci en estudio: Existen pruebas visibles del sobrecruzamiento, los quiasmas observados en meiosis Cuanto más lejos loci más probable que se de sobrecruzamiento entre ellos pr+ F 1 pr pr+ pr vg X vg+ vg Atención, se muestran cromosomas sin replicar
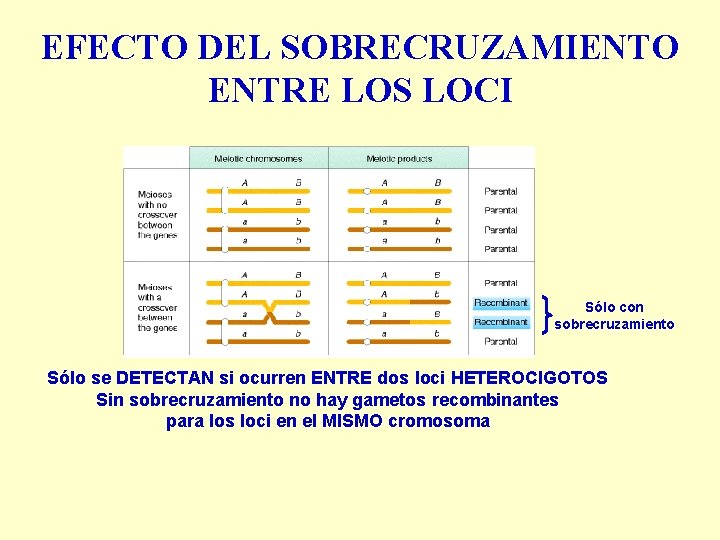
EFECTO DEL SOBRECRUZAMIENTO ENTRE LOS LOCI Sólo con sobrecruzamiento Sólo se DETECTAN si ocurren ENTRE dos loci HETEROCIGOTOS Sin sobrecruzamiento no hay gametos recombinantes para los loci en el MISMO cromosoma

TIPOS DE DIHIBRIDOS DE GENES LIGADOS Ligados en fase de ACOPLAMIENTO Ligados en fase de REPULSIÓN
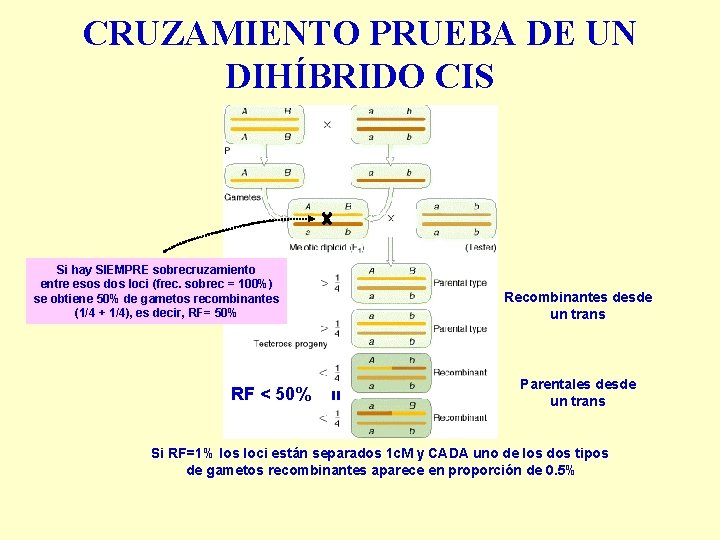
CRUZAMIENTO PRUEBA DE UN DIHÍBRIDO CIS Si hay SIEMPRE sobrecruzamiento entre esos dos loci (frec. sobrec = 100%) se obtiene 50% de gametos recombinantes (1/4 + 1/4), es decir, RF= 50% = RF < 50% Recombinantes desde un trans Parentales desde un trans Si RF=1% los loci están separados 1 c. M y CADA uno de los dos tipos de gametos recombinantes aparece en proporción de 0. 5%

LIGAMIENTO ABSOLUTO El ligamiento absoluto fue descubierto por Bridges en Drosophila P pr+pr+vg+vg+ x prprvgvg F 1 ♀ pr+prvg+vg X ♂ prprvgvg P pr+pr+vg+vg+ x prprvgvg F 1 ♂ pr+prvg+vg X ♀ prprvgvg [pr+vg+] = 1339 [pr+vg+] = 519 [prvg] = 1195 [prvg] = 552 [pr+vg] = 151 [pr+vg] = 0 [prvg+] = 154 [prvg+] = 0 Luego se ha comprobado que el macho de Drosophila es aquiasmático.

¿DEMUESTRAN LOS DATOS QUE HAY LIGAMIENTO? A/A B/B x a/a b/b Parental Recomb. Total A a B b b B 63 58 38 41 200 A/a B/b x a/a b/b Si NO hay ligamiento proporciones 1: 1: 1: 1 Pero puede diferir de esa proporción: -por ligamiento -por mala viabilidad de algún elemento Cosas a comprobar: -1)no hay segregación 1: 1: 1: 1 -2)cada locus segrega normalmente -3)segregan independientemente

¿DEMUESTRAN LOS DATOS QUE HAY LIGAMIENTO? ¿Es segregación 1: 1: 1: 1? Parental Recomb. Total A a B b b B Obs 63 58 38 41 200 Esp 50 50 (O-E)2/E 3. 38 1. 28 2. 88 1. 62 9. 16 c 2 = 9. 16 Nº grados de libertad = 3
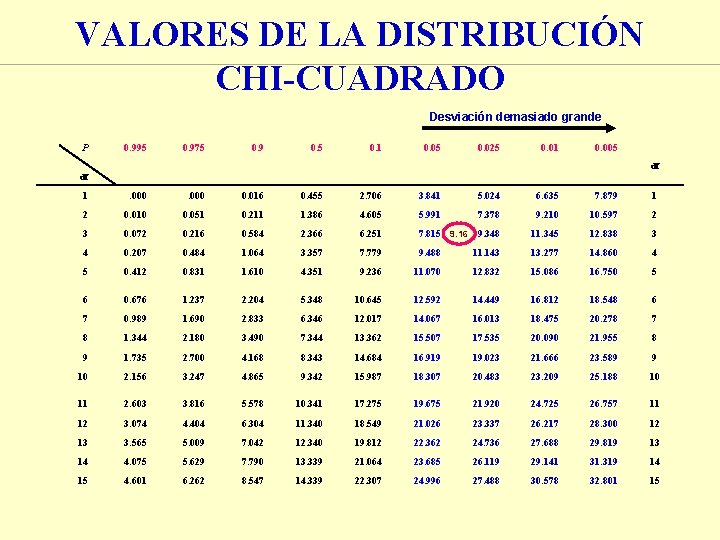
VALORES DE LA DISTRIBUCIÓN CHI-CUADRADO Desviación demasiado grande P 0. 995 0. 975 0. 9 0. 5 0. 1 0. 05 0. 025 0. 01 0. 005 df df 1 . 000 0. 016 0. 455 2. 706 3. 841 5. 024 6. 635 7. 879 1 2 0. 010 0. 051 0. 211 1. 386 4. 605 5. 991 7. 378 9. 210 10. 597 2 3 0. 072 0. 216 0. 584 2. 366 6. 251 7. 815 9. 16 9. 348 11. 345 12. 838 3 4 0. 207 0. 484 1. 064 3. 357 7. 779 9. 488 11. 143 13. 277 14. 860 4 5 0. 412 0. 831 1. 610 4. 351 9. 236 11. 070 12. 832 15. 086 16. 750 5 6 0. 676 1. 237 2. 204 5. 348 10. 645 12. 592 14. 449 16. 812 18. 548 6 7 0. 989 1. 690 2. 833 6. 346 12. 017 14. 067 16. 013 18. 475 20. 278 7 8 1. 344 2. 180 3. 490 7. 344 13. 362 15. 507 17. 535 20. 090 21. 955 8 9 1. 735 2. 700 4. 168 8. 343 14. 684 16. 919 19. 023 21. 666 23. 589 9 10 2. 156 3. 247 4. 865 9. 342 15. 987 18. 307 20. 483 23. 209 25. 188 10 11 2. 603 3. 816 5. 578 10. 341 17. 275 19. 675 21. 920 24. 725 26. 757 11 12 3. 074 4. 404 6. 304 11. 340 18. 549 21. 026 23. 337 26. 217 28. 300 12 13 3. 565 5. 009 7. 042 12. 340 19. 812 22. 362 24. 736 27. 688 29. 819 13 14 4. 075 5. 629 7. 790 13. 339 21. 064 23. 685 26. 119 29. 141 31. 319 14 15 4. 601 6. 262 8. 547 14. 339 22. 307 24. 996 27. 488 30. 578 32. 801 15
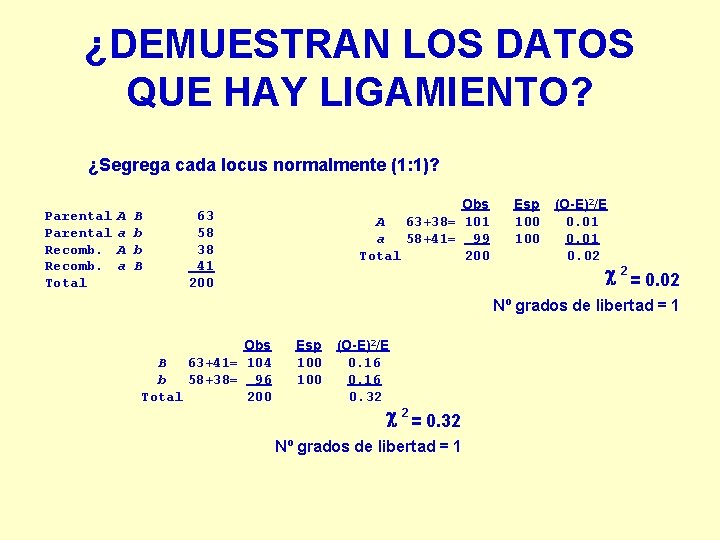
¿DEMUESTRAN LOS DATOS QUE HAY LIGAMIENTO? ¿Segrega cada locus normalmente (1: 1)? Parental Recomb. Total A a B b b B Obs A 63+38= 101 a 58+41= 99 Total 200 63 58 38 41 200 Esp 100 (O-E)2/E 0. 01 0. 02 c 2 = 0. 02 Nº grados de libertad = 1 Obs B 63+41= 104 b 58+38= 96 Total 200 Esp 100 (O-E)2/E 0. 16 0. 32 c 2 = 0. 32 Nº grados de libertad = 1
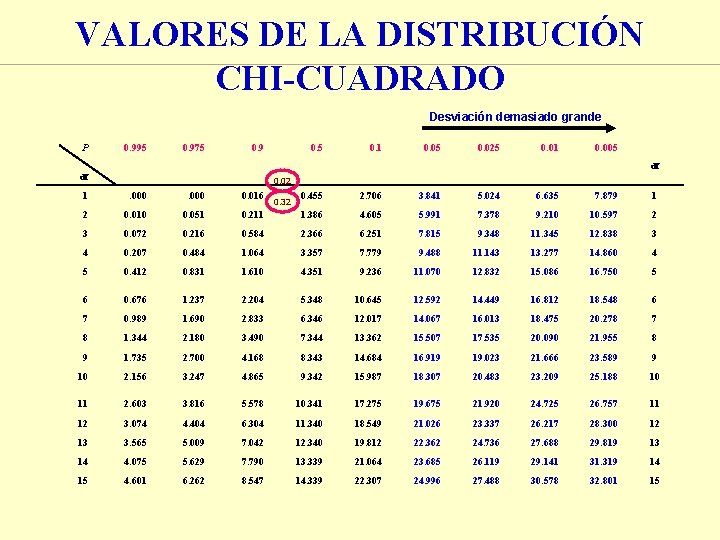
VALORES DE LA DISTRIBUCIÓN CHI-CUADRADO Desviación demasiado grande P 0. 995 0. 975 0. 9 0. 5 0. 1 0. 05 0. 025 0. 01 0. 005 df df 0. 02 1 . 000 0. 016 0. 455 2. 706 3. 841 5. 024 6. 635 7. 879 1 2 0. 010 0. 051 0. 211 1. 386 4. 605 5. 991 7. 378 9. 210 10. 597 2 3 0. 072 0. 216 0. 584 2. 366 6. 251 7. 815 9. 348 11. 345 12. 838 3 4 0. 207 0. 484 1. 064 3. 357 7. 779 9. 488 11. 143 13. 277 14. 860 4 5 0. 412 0. 831 1. 610 4. 351 9. 236 11. 070 12. 832 15. 086 16. 750 5 6 0. 676 1. 237 2. 204 5. 348 10. 645 12. 592 14. 449 16. 812 18. 548 6 7 0. 989 1. 690 2. 833 6. 346 12. 017 14. 067 16. 013 18. 475 20. 278 7 8 1. 344 2. 180 3. 490 7. 344 13. 362 15. 507 17. 535 20. 090 21. 955 8 9 1. 735 2. 700 4. 168 8. 343 14. 684 16. 919 19. 023 21. 666 23. 589 9 10 2. 156 3. 247 4. 865 9. 342 15. 987 18. 307 20. 483 23. 209 25. 188 10 11 2. 603 3. 816 5. 578 10. 341 17. 275 19. 675 21. 920 24. 725 26. 757 11 12 3. 074 4. 404 6. 304 11. 340 18. 549 21. 026 23. 337 26. 217 28. 300 12 13 3. 565 5. 009 7. 042 12. 340 19. 812 22. 362 24. 736 27. 688 29. 819 13 14 4. 075 5. 629 7. 790 13. 339 21. 064 23. 685 26. 119 29. 141 31. 319 14 15 4. 601 6. 262 8. 547 14. 339 22. 307 24. 996 27. 488 30. 578 32. 801 15 0. 32
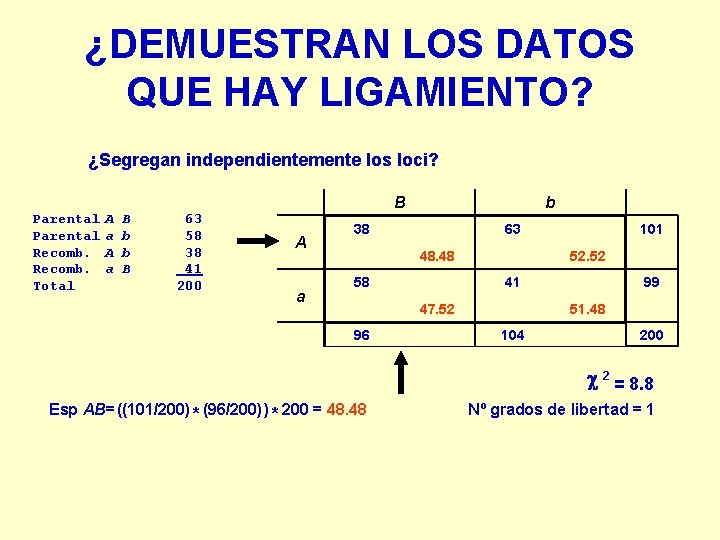
¿DEMUESTRAN LOS DATOS QUE HAY LIGAMIENTO? ¿Segregan independientemente los loci? Parental Recomb. Total A a B b b B 63 58 38 41 200 B A a b 38 63 48. 48 58 52. 52 41 47. 52 96 101 99 51. 48 104 200 c 2 = 8. 8 Esp AB= ((101/200) * (96/200) ) * 200 = 48. 48 Nº grados de libertad = 1
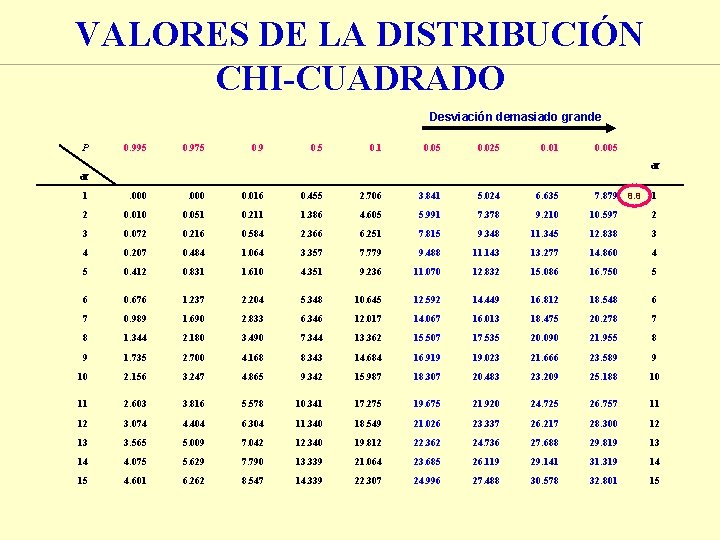
VALORES DE LA DISTRIBUCIÓN CHI-CUADRADO Desviación demasiado grande P 0. 995 0. 975 0. 9 0. 5 0. 1 0. 05 0. 025 0. 01 0. 005 df df 1 . 000 0. 016 0. 455 2. 706 3. 841 5. 024 6. 635 7. 879 2 0. 010 0. 051 0. 211 1. 386 4. 605 5. 991 7. 378 9. 210 10. 597 2 3 0. 072 0. 216 0. 584 2. 366 6. 251 7. 815 9. 348 11. 345 12. 838 3 4 0. 207 0. 484 1. 064 3. 357 7. 779 9. 488 11. 143 13. 277 14. 860 4 5 0. 412 0. 831 1. 610 4. 351 9. 236 11. 070 12. 832 15. 086 16. 750 5 6 0. 676 1. 237 2. 204 5. 348 10. 645 12. 592 14. 449 16. 812 18. 548 6 7 0. 989 1. 690 2. 833 6. 346 12. 017 14. 067 16. 013 18. 475 20. 278 7 8 1. 344 2. 180 3. 490 7. 344 13. 362 15. 507 17. 535 20. 090 21. 955 8 9 1. 735 2. 700 4. 168 8. 343 14. 684 16. 919 19. 023 21. 666 23. 589 9 10 2. 156 3. 247 4. 865 9. 342 15. 987 18. 307 20. 483 23. 209 25. 188 10 11 2. 603 3. 816 5. 578 10. 341 17. 275 19. 675 21. 920 24. 725 26. 757 11 12 3. 074 4. 404 6. 304 11. 340 18. 549 21. 026 23. 337 26. 217 28. 300 12 13 3. 565 5. 009 7. 042 12. 340 19. 812 22. 362 24. 736 27. 688 29. 819 13 14 4. 075 5. 629 7. 790 13. 339 21. 064 23. 685 26. 119 29. 141 31. 319 14 15 4. 601 6. 262 8. 547 14. 339 22. 307 24. 996 27. 488 30. 578 32. 801 15 8. 8 1
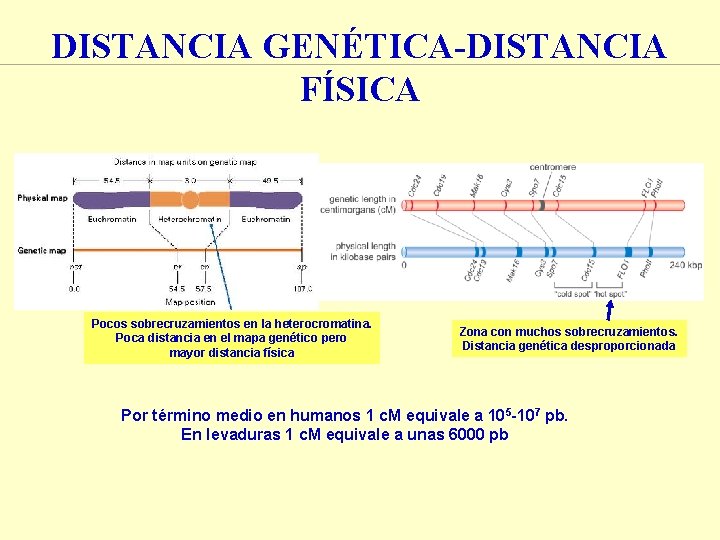
DISTANCIA GENÉTICA-DISTANCIA FÍSICA Pocos sobrecruzamientos en la heterocromatina. Poca distancia en el mapa genético pero mayor distancia física Zona con muchos sobrecruzamientos. Distancia genética desproporcionada Por término medio en humanos 1 c. M equivale a 105 -107 pb. En levaduras 1 c. M equivale a unas 6000 pb
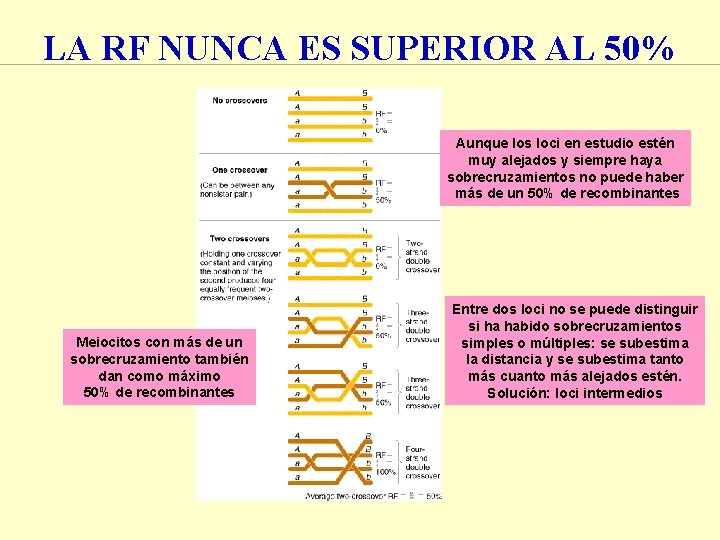
LA RF NUNCA ES SUPERIOR AL 50% Aunque los loci en estudio estén muy alejados y siempre haya sobrecruzamientos no puede haber más de un 50% de recombinantes Meiocitos con más de un sobrecruzamiento también dan como máximo 50% de recombinantes Entre dos loci no se puede distinguir si ha habido sobrecruzamientos simples o múltiples: se subestima la distancia y se subestima tanto más cuanto más alejados estén. Solución: loci intermedios

PROBLEMA DE TRES PUNTOS LOCI EN ESTUDIO: v (ojos bermellón), v+ (ojos rojos) cv (alas sin venas transv. ), cv+ (con venas transv. ) ct (alas borde hendido, ct+ (alas borde liso) v+ cv ct / v+ cv ct x v cv+ ct+ / v cv+ ct+ v+ cv ct / v cv+ ct+ x v cv ct / v cv ct Pareja v/cv. Recombinantes: v cv y v+ cv+ 45 + 40 + 89 + 94 = 268, RF= 18. 5% Pareja v/ct. Recombinantes: v ct y v+ ct+ 89 + 94 +3 +5 = 191, RF= 13. 2% Pareja ct/cv. Recombinantes: cv ct+ y cv+ ct 45 + 40 +3 +5 = 93, RF= 6. 4% 13. 2 + 6. 4 = 19. 6 > 18. 5

PROBLEMA DE TRES PUNTOS 13. 2 + 6. 4 = 19. 6 > 18. 5 Pareja v/cv. Recombinantes: 45 + 40 + 89 + 94 + 2 x 3 + 2 x 5 = 284, RF= 19. 6% Cuanto más alejados estén los loci en estudio más se subestima la distancia entre ellos No se hubieran detectado de no ser por el locus intermedio

PROBLEMA DE TRES PUNTOS COECIFIENTE DE COINCIDENCIA (cdc) = dobles recomb obs / dobles recomb esper INTERFERENCIA = 1 - cdc DOBLES ESPERADOS = 0. 132 x 0. 064 = 0. 0084 x 1448 = 12 DOBLES OBSERVADOS = 8 I = 1 – 8/12 = 1/3 Rango de valores de I: I = 0, mismo número obs. que esperados 0 < I < 1, rango normal I = 1, no hay dobles recomb. I > 0, más dobles recomb. de lo esperado

MAPAS GENÉTICOS En ellos una serie de genes y cualquier tipo de marcador aparecen ordenados y separados por distancias genéticas Un mapa “saturado” tiene una GRAN CANTIDAD de genes o marcadores separados entre si por pocos c. M y distribuidos por todo el genoma Aquellos genes y marcadores ligados forman un “grupo de ligamiento”. En un mapa saturado el número de grupos de ligamiento coincidirá con el de cromosomas Para asignar los grupos de ligamiento a cromosomas individuales se precisan técnicas de otro tipo El primer mapa genético lo elaboró Sturtevant en 1911 para el cromosoma X de Drosophila
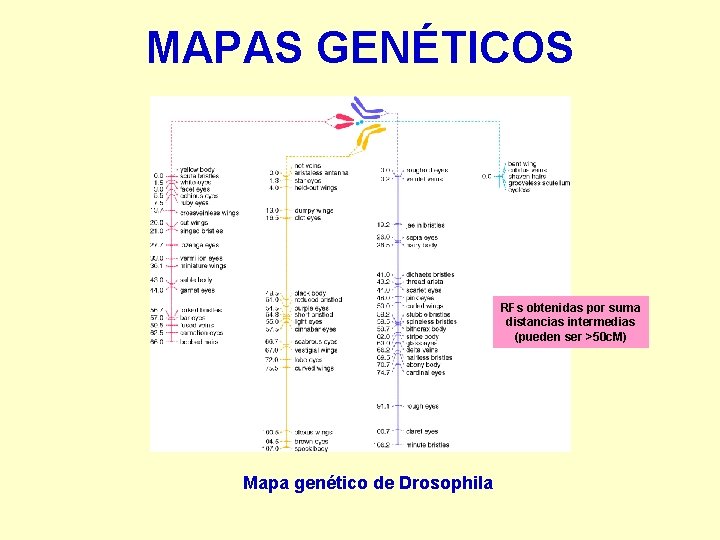
MAPAS GENÉTICOS RFs obtenidas por suma distancias intermedias (pueden ser >50 c. M) Mapa genético de Drosophila
- Slides: 25