Leccin 12 Evolucin molecular LECCIN 12 1 Cambios

Lección 12 Evolución molecular

LECCIÓN 12 • • • 1) Cambios de secuencia y consecuencias funcionales 2) ¿Papel de la epigenética? 3) Similitud, homología, ortólogos y parálogos 4) Cambios sinónimos y no sinónimos 5) Redes de genes y evolución

LECCIÓN 12 • 1) Cambios de secuencia y consecuencias funcionales • • 2) ¿Papel de la epigenética? 3) Similitud, homología, ortólogos y parálogos 4) Cambios sinónimos y no sinónimos 5) Redes de genes y evolución
¿DÓNDE CAMBIA LA SECUENCIA? Los cambios pueden tener lugar en las regiones codificantes de los genes (CDS), en sus promotores, en zonas importantes para la estructura de la cromatina, para la actividad de los cromosomas … El problema es ser capaces de predecir sus consecuencias funcionales. Más fácil donde mejor se comprenda su funcionamiento: las regiones codificantes de los genes para proteínas. Eso NO quiere decir que los cambios de secuencia en otras partes sean triviales
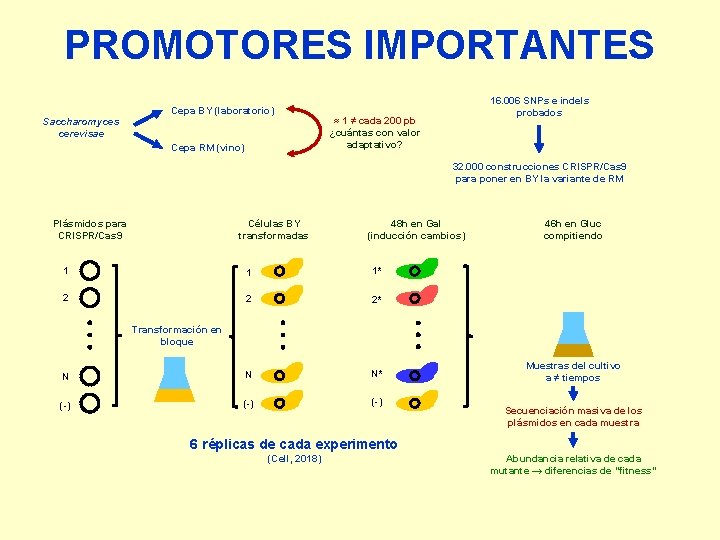
PROMOTORES IMPORTANTES Saccharomyces cerevisae Cepa BY (laboratorio) Cepa RM (vino) 16. 006 SNPs e indels probados ≈ 1 ≠ cada 200 pb ¿cuántas con valor adaptativo? 32. 000 construcciones CRISPR/Cas 9 para poner en BY la variante de RM Plásmidos para CRISPR/Cas 9 Células BY transformadas 48 h en Gal (inducción cambios) 1 1 1* 2 2 2* N N N* (-) (-) 46 h en Gluc compitiendo Transformación en bloque Muestras del cultivo a ≠ tiempos Secuenciación masiva de los plásmidos en cada muestra 6 réplicas de cada experimento (Cell, 2018) Abundancia relativa de cada mutante → diferencias de “fitness”
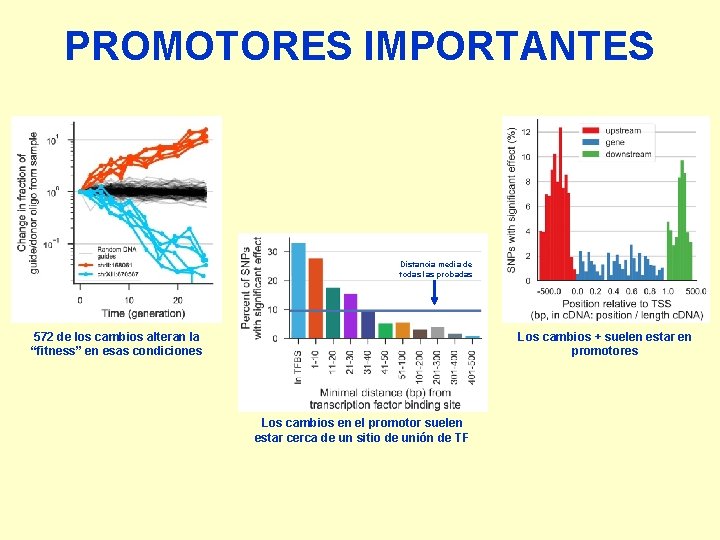
PROMOTORES IMPORTANTES Distancia media de todas las probadas 572 de los cambios alteran la “fitness” en esas condiciones Los cambios + suelen estar en promotores Los cambios en el promotor suelen estar cerca de un sitio de unión de TF
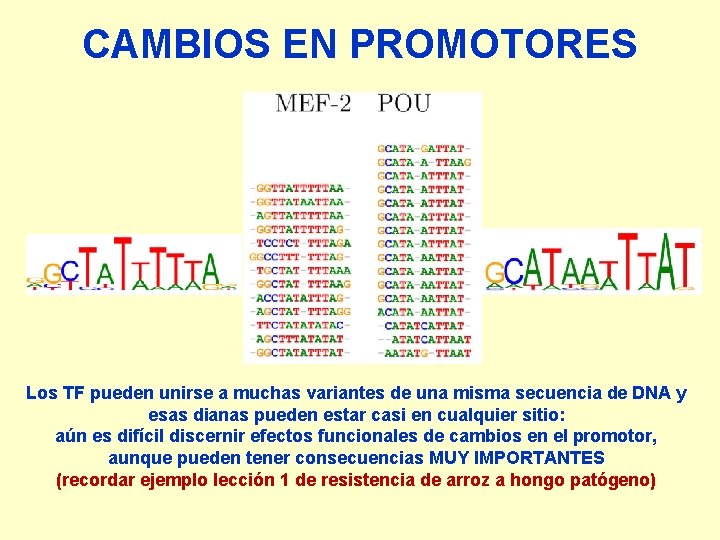
CAMBIOS EN PROMOTORES Los TF pueden unirse a muchas variantes de una misma secuencia de DNA y esas dianas pueden estar casi en cualquier sitio: aún es difícil discernir efectos funcionales de cambios en el promotor, aunque pueden tener consecuencias MUY IMPORTANTES (recordar ejemplo lección 1 de resistencia de arroz a hongo patógeno)
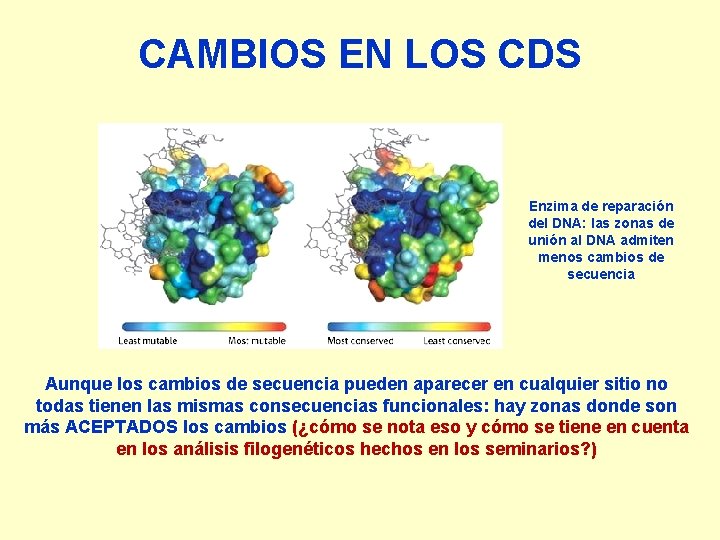
CAMBIOS EN LOS CDS Enzima de reparación del DNA: las zonas de unión al DNA admiten menos cambios de secuencia Aunque los cambios de secuencia pueden aparecer en cualquier sitio no todas tienen las mismas consecuencias funcionales: hay zonas donde son más ACEPTADOS los cambios (¿cómo se nota eso y cómo se tiene en cuenta en los análisis filogenéticos hechos en los seminarios? )
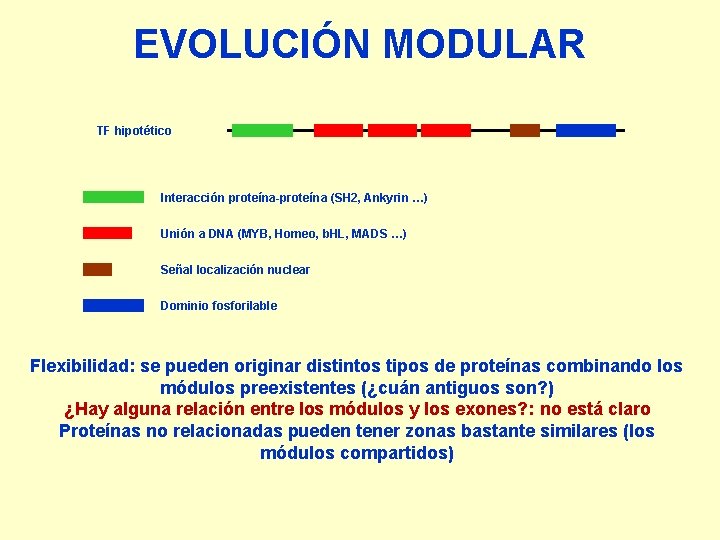
EVOLUCIÓN MODULAR TF hipotético Interacción proteína-proteína (SH 2, Ankyrin …) Unión a DNA (MYB, Homeo, b. HL, MADS …) Señal localización nuclear Dominio fosforilable Flexibilidad: se pueden originar distintos tipos de proteínas combinando los módulos preexistentes (¿cuán antiguos son? ) ¿Hay alguna relación entre los módulos y los exones? : no está claro Proteínas no relacionadas pueden tener zonas bastante similares (los módulos compartidos)

LECCIÓN 12 • 1) Cambios de secuencia y consecuencias funcionales • 2) ¿Papel de la epigenética? • 3) Similitud, homología, ortólogos y parálogos • 4) Cambios sinónimos y no sinónimos • 5) Redes de genes y evolución
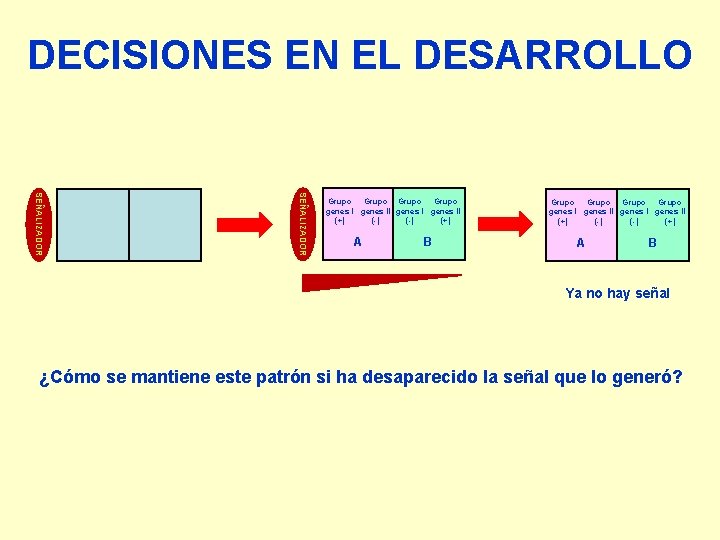
DECISIONES EN EL DESARROLLO SEÑALIZADOR Grupo Grupo genes I genes II (+) (-) (-) (+) A B Ya no hay señal ¿Cómo se mantiene este patrón si ha desaparecido la señal que lo generó?
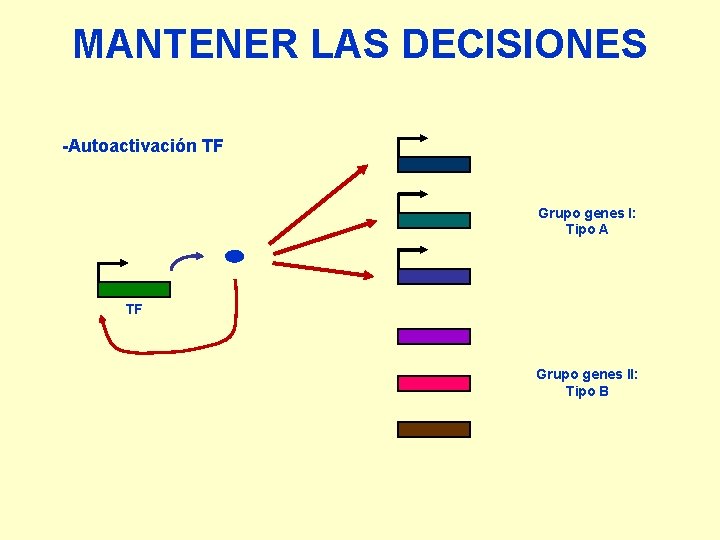
MANTENER LAS DECISIONES -Autoactivación TF Grupo genes I: Tipo A TF Grupo genes II: Tipo B
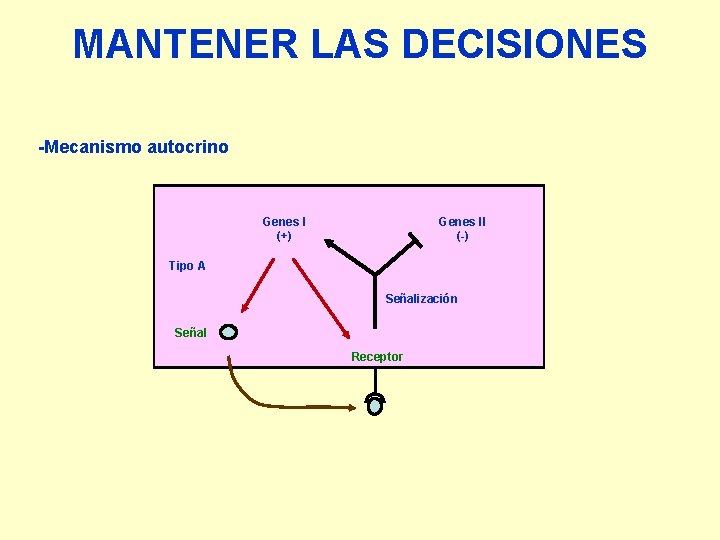
MANTENER LAS DECISIONES -Mecanismo autocrino Genes I (+) Genes II (-) Tipo A Señalización Señal Receptor
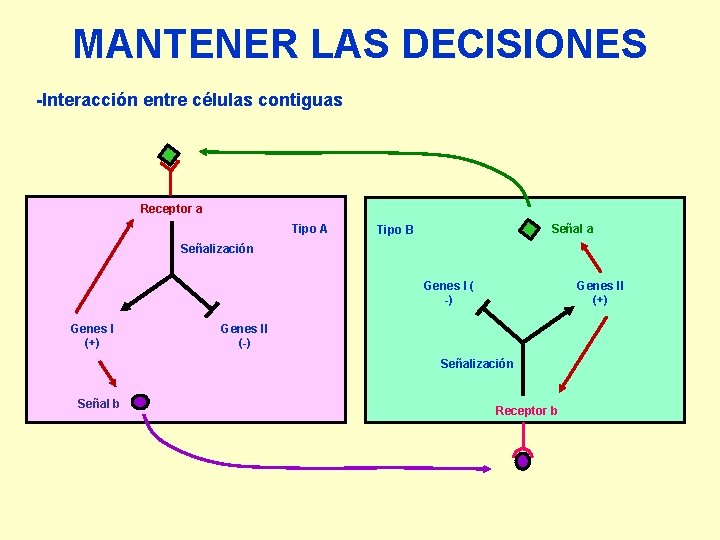
MANTENER LAS DECISIONES -Interacción entre células contiguas Receptor a Tipo A Señal a Tipo B Señalización Genes I ( -) Genes I (+) Genes II (-) Señalización Señal b Receptor b
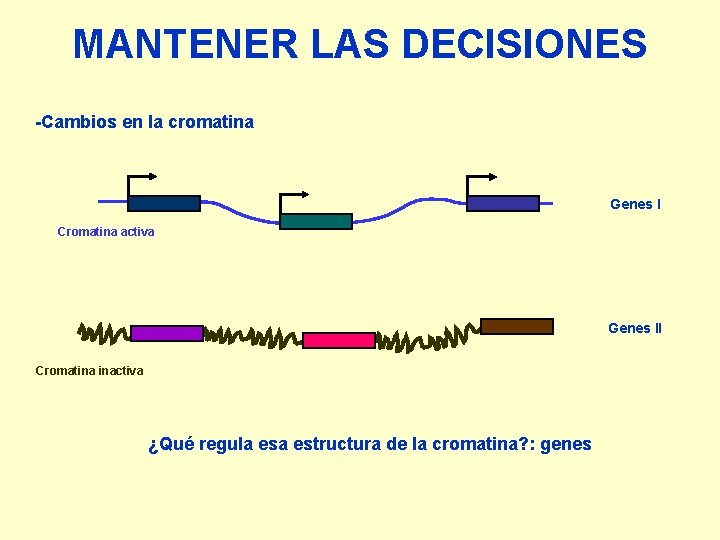
MANTENER LAS DECISIONES -Cambios en la cromatina Genes I Cromatina activa Genes II Cromatina inactiva ¿Qué regula estructura de la cromatina? : genes
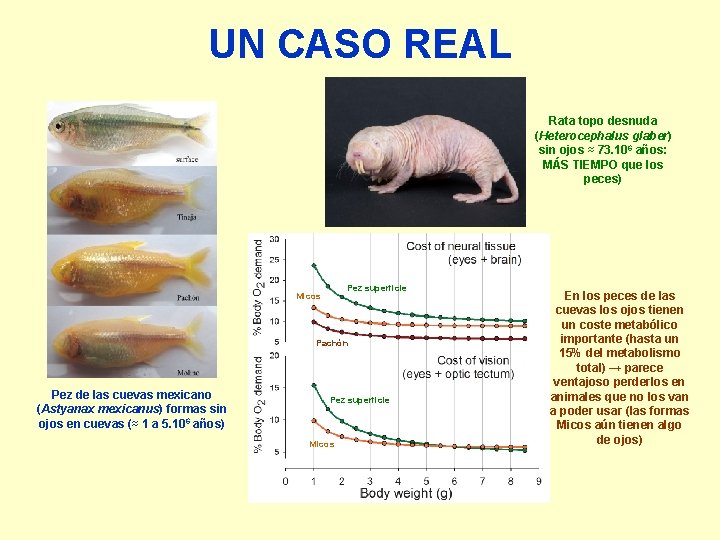
UN CASO REAL Rata topo desnuda (Heterocephalus glaber) sin ojos ≈ 73. 106 años: MÁS TIEMPO que los peces) Pez superficie Micos Pachón Pez de las cuevas mexicano (Astyanax mexicanus) formas sin ojos en cuevas (≈ 1 a 5. 106 años) Pez superficie Micos En los peces de las cuevas los ojos tienen un coste metabólico importante (hasta un 15% del metabolismo total) → parece ventajoso perderlos en animales que no los van a poder usar (las formas Micos aún tienen algo de ojos)
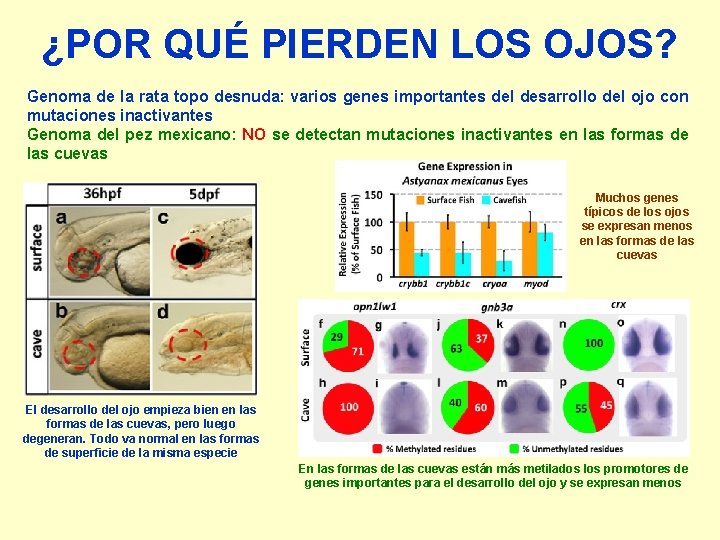
¿POR QUÉ PIERDEN LOS OJOS? Genoma de la rata topo desnuda: varios genes importantes del desarrollo del ojo con mutaciones inactivantes Genoma del pez mexicano: NO se detectan mutaciones inactivantes en las formas de las cuevas Muchos genes típicos de los ojos se expresan menos en las formas de las cuevas El desarrollo del ojo empieza bien en las formas de las cuevas, pero luego degeneran. Todo va normal en las formas de superficie de la misma especie En las formas de las cuevas están más metilados los promotores de genes importantes para el desarrollo del ojo y se expresan menos
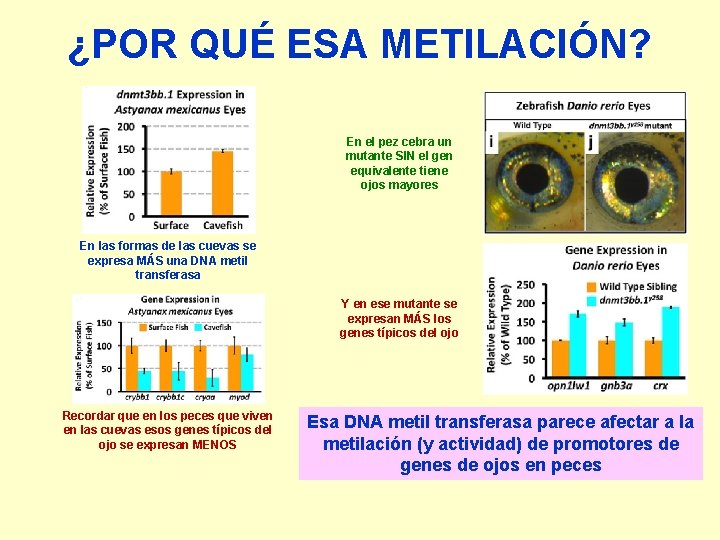
¿POR QUÉ ESA METILACIÓN? En el pez cebra un mutante SIN el gen equivalente tiene ojos mayores En las formas de las cuevas se expresa MÁS una DNA metil transferasa Y en ese mutante se expresan MÁS los genes típicos del ojo Recordar que en los peces que viven en las cuevas esos genes típicos del ojo se expresan MENOS Esa DNA metil transferasa parece afectar a la metilación (y actividad) de promotores de genes de ojos en peces
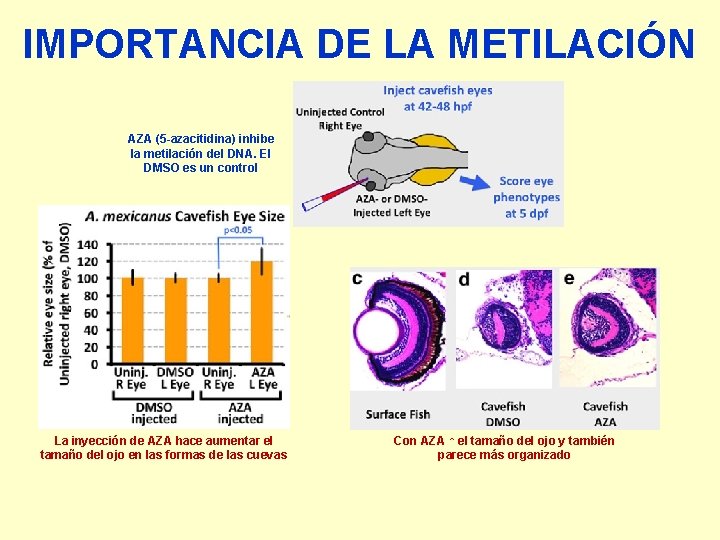
IMPORTANCIA DE LA METILACIÓN AZA (5 -azacitidina) inhibe la metilación del DNA. El DMSO es un control La inyección de AZA hace aumentar el tamaño del ojo en las formas de las cuevas Con AZA ↑ el tamaño del ojo y también parece más organizado
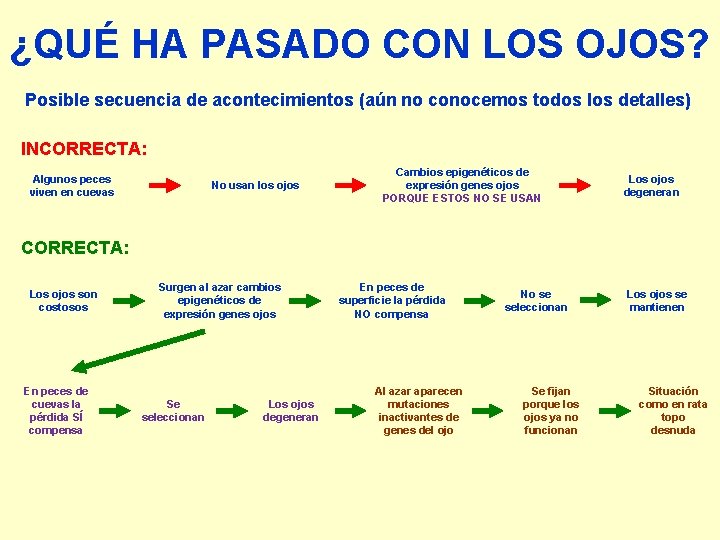
¿QUÉ HA PASADO CON LOS OJOS? Posible secuencia de acontecimientos (aún no conocemos todos los detalles) INCORRECTA: Algunos peces viven en cuevas No usan los ojos Cambios epigenéticos de expresión genes ojos PORQUE ESTOS NO SE USAN Los ojos degeneran CORRECTA: Los ojos son costosos En peces de cuevas la pérdida SÍ compensa Surgen al azar cambios epigenéticos de expresión genes ojos Se seleccionan Los ojos degeneran En peces de superficie la pérdida NO compensa Al azar aparecen mutaciones inactivantes de genes del ojo No se seleccionan Se fijan porque los ojos ya no funcionan Los ojos se mantienen Situación como en rata topo desnuda

¿Y ESO DE LA EPIGENÉTICA? El cambio epigenético podría permitir alterar la expresión de muchos genes típicos del ojo a la vez → facilita su pérdida rápida PERO ese cambio depende probablemente de algún cambio en la secuencia del promotor del gen de la DNA metil transferasa que ↑ su actividad CONSECUENCIA: probablemente sigue teniendo que haber un cambio de secuencia La epigenética es un importante mecanismo de regulación, ¿pero no se estará exagerando en general un poco con ella? : reflexionar sobre esto

LECCIÓN 12 • 1) Cambios de secuencia y consecuencias funcionales • 2) ¿Papel de la epigenética? • 3) Similitud, homología, ortólogos y parálogos • 4) Cambios sinónimos y no sinónimos • 5) Redes de genes y evolución
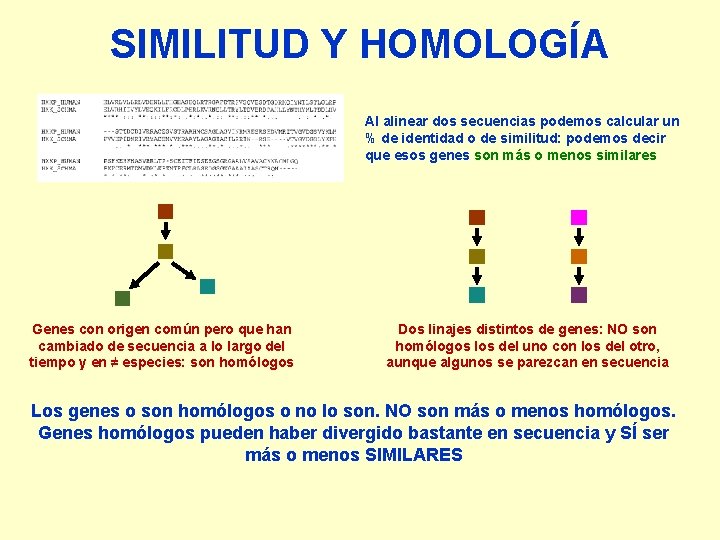
SIMILITUD Y HOMOLOGÍA Al alinear dos secuencias podemos calcular un % de identidad o de similitud: podemos decir que esos genes son más o menos similares Genes con origen común pero que han cambiado de secuencia a lo largo del tiempo y en ≠ especies: son homólogos Dos linajes distintos de genes: NO son homólogos los del uno con los del otro, aunque algunos se parezcan en secuencia Los genes o son homólogos o no lo son. NO son más o menos homólogos. Genes homólogos pueden haber divergido bastante en secuencia y SÍ ser más o menos SIMILARES
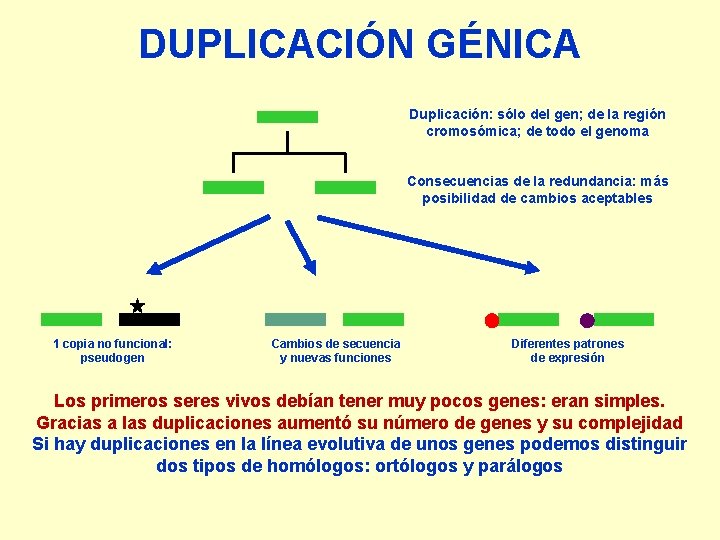
DUPLICACIÓN GÉNICA Duplicación: sólo del gen; de la región cromosómica; de todo el genoma Consecuencias de la redundancia: más posibilidad de cambios aceptables 1 copia no funcional: pseudogen Cambios de secuencia y nuevas funciones Diferentes patrones de expresión Los primeros seres vivos debían tener muy pocos genes: eran simples. Gracias a las duplicaciones aumentó su número de genes y su complejidad Si hay duplicaciones en la línea evolutiva de unos genes podemos distinguir dos tipos de homólogos: ortólogos y parálogos
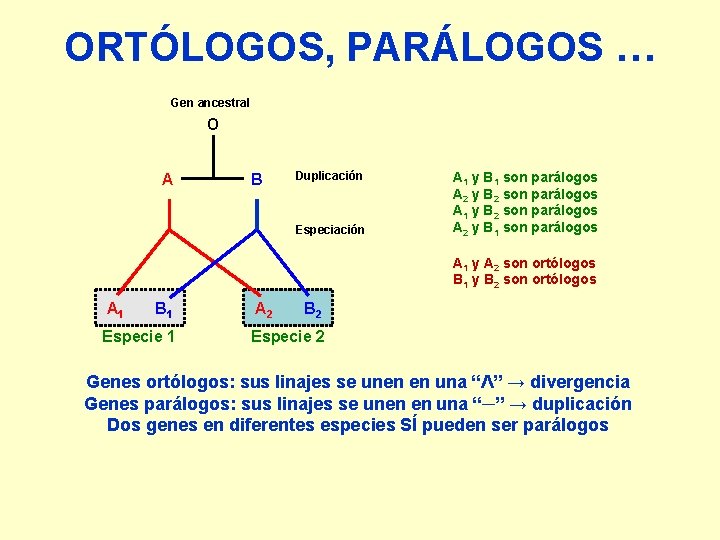
ORTÓLOGOS, PARÁLOGOS … Gen ancestral O A B Duplicación Especiación A 1 y B 1 son parálogos A 2 y B 2 son parálogos A 1 y B 2 son parálogos A 2 y B 1 son parálogos A 1 y A 2 son ortólogos B 1 y B 2 son ortólogos A 1 B 1 Especie 1 A 2 B 2 Especie 2 Genes ortólogos: sus linajes se unen en una “Ʌ” → divergencia Genes parálogos: sus linajes se unen en una “─” → duplicación Dos genes en diferentes especies SÍ pueden ser parálogos
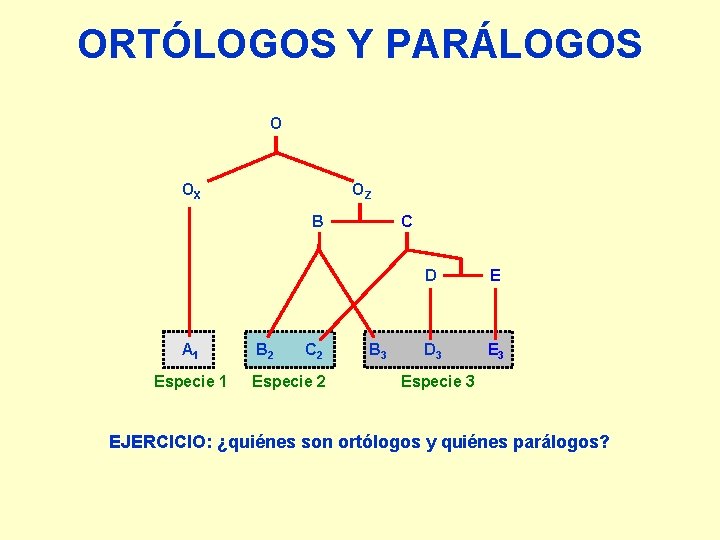
ORTÓLOGOS Y PARÁLOGOS O OX OZ B A 1 Especie 1 B 2 C 2 Especie 2 C B 3 D E D 3 Especie 3 EJERCICIO: ¿quiénes son ortólogos y quiénes parálogos?

LECCIÓN 12 • 1) Cambios de secuencia y consecuencias funcionales • 2) ¿Papel de la epigenética? • 3) Similitud, homología, ortólogos y parálogos • 4) Cambios sinónimos y no sinónimos • 5) Redes de genes y evolución

SELECCIÓN Y SECUENCIAS Una clasificación de las variantes en el genoma: -Ventajosas (favorables para el individuo que las porta) → sujetas a selección positiva (tenderá a fijarlas en la población) -Deletéreas (desfavorables para el individuo que las porta) → sujetas a selección negativa o purificadora (tenderá a eliminarlas de la población) -Neutras (afectan muy poco o nada al individuo que las porta) → sujetas a la deriva (las típicas estarán en regiones no codificantes y sin función) OBJETIVO: si comparamos las secuencias de genes homólogos en diferentes especies -¿podemos detectar si hay líneas evolutivas entre esas especies en que haya primado más la selección +, la – o la deriva? -¿podemos detectar zonas en el gen que hayan estado más sujetas a la selección +, la – o la deriva? Método para responder basado en el análisis de las secuencias de nucleótidos en regiones CODIFICANTES de los genes: estimar el cociente entre cambios NO sinónimos y sinónimos

TIPOS DE CAMBIO Y SELECCIÓN Cambio no sinónimo: el cambio de nt SÍ causa cambio de aa Cambio sinónimo (o silencioso): el cambio de nt NO causa cambio de aa FUNDAMENTO: -Cabe esperar que los cambios sinónimos sean invisibles a la selección → su frecuencia indica fuerza de la deriva en la línea que ha llevado de un gen al otro -Si en la línea que ha llevado de un gen al otro sólo ha habido deriva, los cambios NO sinónimos se habrán mantenido con ≈ frecuencia → cociente NO SINOM/SINOM ≈ 1 -Si en la línea que ha llevado de un gen al otro ha habido bastante selección positiva, los cambios NO sinónimos se habrán mantenido con > frecuencia → cociente NO SINOM/SINOM > 1 -Si en la línea que ha llevado de un gen al otro ha habido bastante selección negativa, los cambios NO sinónimos se habrán tendido a eliminar → cociente NO SINOM/SINOM < 1

¿CÓMO CALCULARLO? Sec 1 Sec 2 Asp Thr Ala Val GAC ACA GCG GTT GCC ACT TCG GTT Ala Thr Ser Val Cambios NO sinónimos: 2 Cambios sinónimos: 1 ¿Cociente N/S = 2? ENGAÑOSO: porque el código genético ofrece distintas posibilidades de cambios sinónimos y no sinónimos y porque, en particular, eso depende de los aas que haya en la zona comparada (en una con muchas Leu hay más oportunidades de cambio sinónimo que en otra con muchas Lys) Hay que tener en cuenta el número de sitios en los que PODRÍA HABER cambios sinónimos y no sinónimos en la región comparada: d. N = nº cambios NO sinónimos/nº sitios donde podría haberlos d. S = nº cambios sinónimos/nº sitios donde podría haberlos ω = d. N/d. S ω < 1 sugiere selección negativa o purificadora ω ≈ 1 sugiere que ha primado la deriva ω > 1 sugiere selección positiva

UN CASO MUY SIMPLE Sec 1 GTT Asp Thr Ala Val GAC ACA GCG 112 114 114 Sec 1 GTT Sec 2 Asp Thr Ala Val GAC ACA GCG TIPOS DE SITIOS 1: cualquier cambio de nt es NO sinónimo 2: dos cambios de nt son NO sinónimos 4: ningún cambio de nt es NO sinónimo Cambios NO sinónimos: 2 Cambios sinónimos: 1 GCC ACT TCG GTT Ala Thr Ser Val Se puede estimar que en esta zona hay: -Sitios donde podrían darse cambios no sinónimos: 8, 33 -Sitios donde podrían darse cambios sinónimos: 3, 67 Por tanto: -d. N = 2/8, 33 = 0, 24 -d. S = 1/3, 67 = 0, 27 ω = 0, 24/0, 27 = 0, 89 < 1 aunque hay más cambios no sinónimos

HAY MÁS COMPLICACIONES Otras cosas a tener en cuenta para el cálculo: -Afecta el que haya diferentes frecuencias de transiciones y transversiones -Si los codones alineados difieren en más de 1 nt hay varios posibles caminos para llegar del uno al otro y eso hay que tenerlo en cuenta -Afecta si no todos los codones se usan con igual frecuencia Hay diversos métodos y programas que permiten hacer estimaciones de ω y su significación estadística. Información y un útil paquete de programas pueden descargarse en la dirección: http: //abacus. gene. ucl. ac. uk/software/paml. html
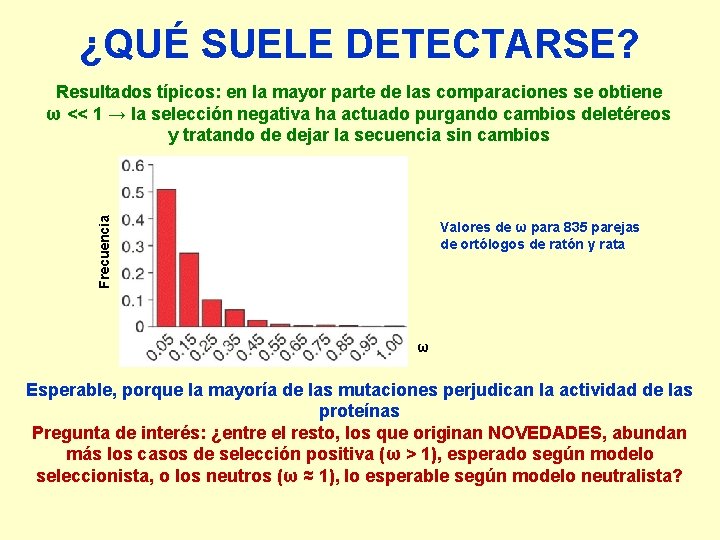
¿QUÉ SUELE DETECTARSE? Frecuencia Resultados típicos: en la mayor parte de las comparaciones se obtiene ω << 1 → la selección negativa ha actuado purgando cambios deletéreos y tratando de dejar la secuencia sin cambios Valores de ω para 835 parejas de ortólogos de ratón y rata ω Esperable, porque la mayoría de las mutaciones perjudican la actividad de las proteínas Pregunta de interés: ¿entre el resto, los que originan NOVEDADES, abundan más los casos de selección positiva (ω > 1), esperado según modelo seleccionista, o los neutros (ω ≈ 1), lo esperable según modelo neutralista?

¿SELECCIÓN O DERIVA? Probabilidad GRAN DIFICULTAD: ω es un promedio de toda la secuencia → si sólo unas posiciones están sujetas a selección + mientras que el resto lo está a negativa o neutra apenas nunca obtendremos un ω > 1 INTENTO DE SOLUCIÓN: métodos que tratan de estimar ω para CADA codón entre las proteínas en comparación Datos de genes de una proteína de reconocimiento de gametos en 25 especies de moluscos Probabilidad de pertenecer a las clases: ω = 0, 085 ω = 0, 911 ω = 3, 065 Detectan sitios sujetos a selección positiva pero aún son poco sensibles (ω son ahora promedios a partir de las secuencias en varias especies)
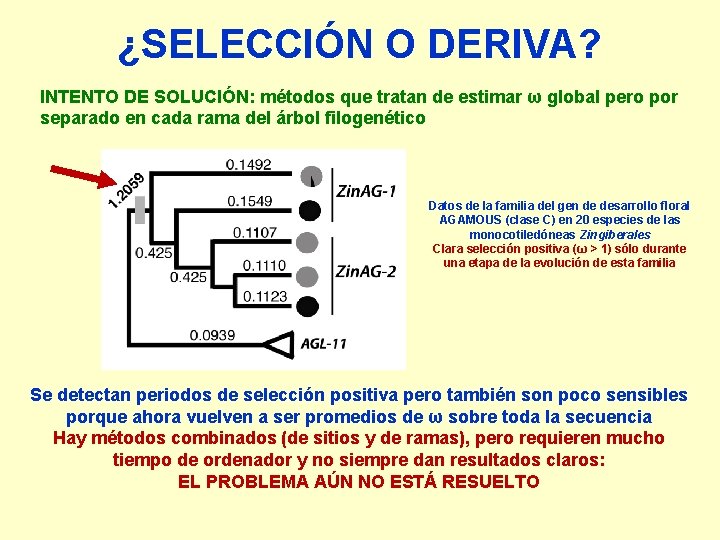
¿SELECCIÓN O DERIVA? INTENTO DE SOLUCIÓN: métodos que tratan de estimar ω global pero por separado en cada rama del árbol filogenético Datos de la familia del gen de desarrollo floral AGAMOUS (clase C) en 20 especies de las monocotiledóneas Zingiberales Clara selección positiva (ω > 1) sólo durante una etapa de la evolución de esta familia Se detectan periodos de selección positiva pero también son poco sensibles porque ahora vuelven a ser promedios de ω sobre toda la secuencia Hay métodos combinados (de sitios y de ramas), pero requieren mucho tiempo de ordenador y no siempre dan resultados claros: EL PROBLEMA AÚN NO ESTÁ RESUELTO

LECCIÓN 12 • • 1) Cambios de secuencia y consecuencias funcionales 2) ¿Papel de la epigenética? 3) Similitud, homología, ortólogos y parálogos 4) Cambios sinónimos y no sinónimos • 5) Redes de genes y evolución
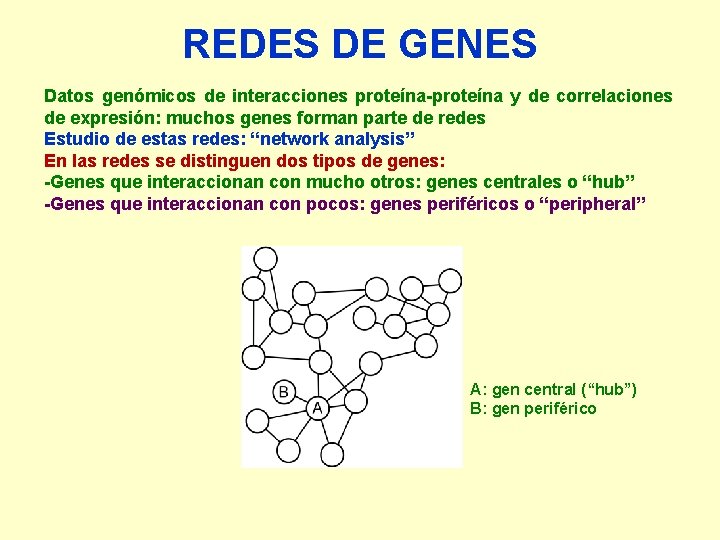
REDES DE GENES Datos genómicos de interacciones proteína-proteína y de correlaciones de expresión: muchos genes forman parte de redes Estudio de estas redes: “network analysis” En las redes se distinguen dos tipos de genes: -Genes que interaccionan con mucho otros: genes centrales o “hub” -Genes que interaccionan con pocos: genes periféricos o “peripheral” A: gen central (“hub”) B: gen periférico
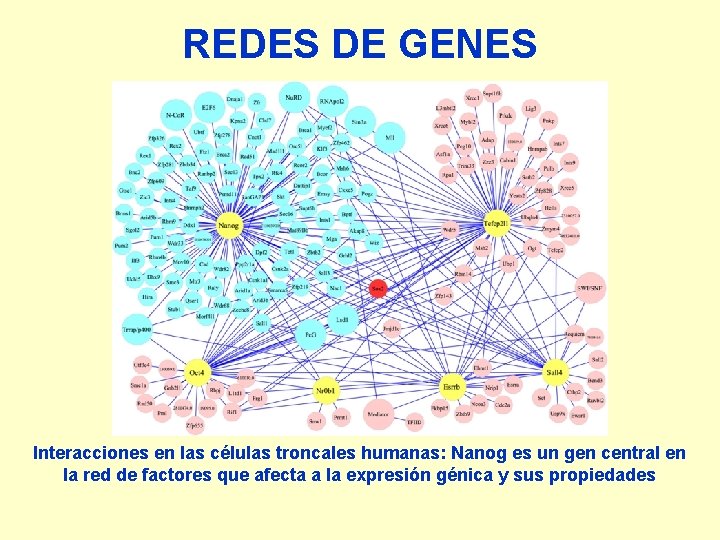
REDES DE GENES Interacciones en las células troncales humanas: Nanog es un gen central en la red de factores que afecta a la expresión génica y sus propiedades
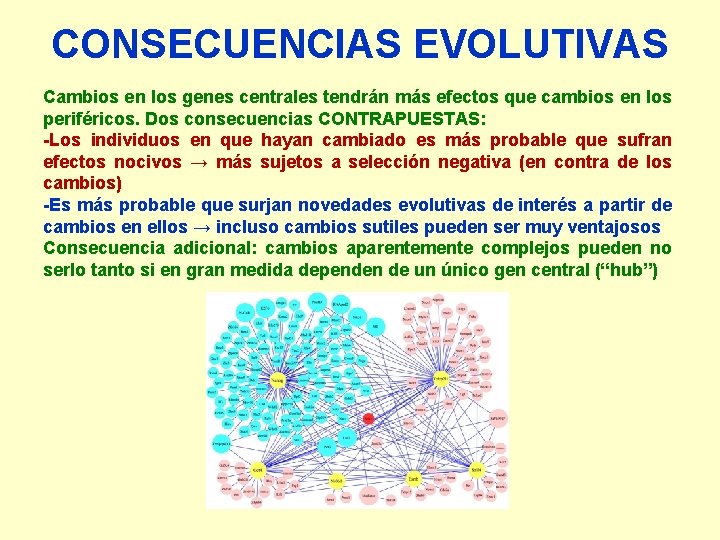
CONSECUENCIAS EVOLUTIVAS Cambios en los genes centrales tendrán más efectos que cambios en los periféricos. Dos consecuencias CONTRAPUESTAS: -Los individuos en que hayan cambiado es más probable que sufran efectos nocivos → más sujetos a selección negativa (en contra de los cambios) -Es más probable que surjan novedades evolutivas de interés a partir de cambios en ellos → incluso cambios sutiles pueden ser muy ventajosos Consecuencia adicional: cambios aparentemente complejos pueden no serlo tanto si en gran medida dependen de un único gen central (“hub”)
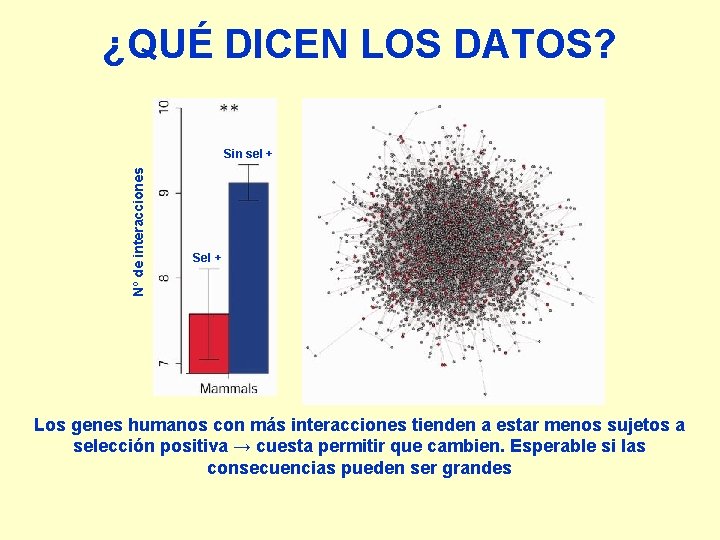
¿QUÉ DICEN LOS DATOS? Nº de interacciones Sin sel + Sel + Los genes humanos con más interacciones tienden a estar menos sujetos a selección positiva → cuesta permitir que cambien. Esperable si las consecuencias pueden ser grandes

Algunas cosas que conviene tener claras al final de esta lección

- Se suelen estudiar más los cambios de secuencia en los CDS porque son más fáciles de predecir sus consecuencias funcionales, no porque sean los únicos de interés → sobre todo los de los promotores - Muchas proteínas están organizadas en módulos compartidos con otras - Los cambios epigenéticos pueden ser importantes en la evolución, pero al final su efecto depende de cambios en secuencias de genes - Importancia de las duplicaciones en la evolución. Distinguir entre genes ortólogos y parálogos. Distinguir entre homología y similitud - Variantes ventajosas: sujetas a selección +. Variantes deletéreas: sujetas a selección -. Variantes neutras (o casi): sujetas a deriva - Distinguir cambios sinónimos y d. S, cambios no sinónimos y d. N - Cálculo de ω. Si ω>1 posible selección positiva; si <1 posible selección negativa; si ≈1 posible deriva. Complicaciones del cálculo de ω - Genes centrales y periféricos en las redes de genes. Los centrales suelen estar más conservados, pero sutiles cambios en ellos pueden ser importantes para la evolución
- Slides: 42