Introduccin a los Algoritmos Genticos en Biologa ALGORITMOS

Introducción a los Algoritmos Genéticos en Biología

ALGORITMOS GENÉTICOS Día 1

¿Qué son? Son algoritmos de búsqueda de soluciones basados en la mecánica de la selección natural y la genética de poblaciones

Idea base Tenemos un problema a resolver.

Idea base Generamos una “población” de posibles soluciones a ese problema.

Idea base Asignamos a cada solución un valor de eficacia (“fitness”).

Idea base Las soluciones pueden recombinar y mutar (evolucionan).

Idea base Dejamos actuar a la evolución via la selección natural para que encuentre la mejor solución (resuelva el problema).
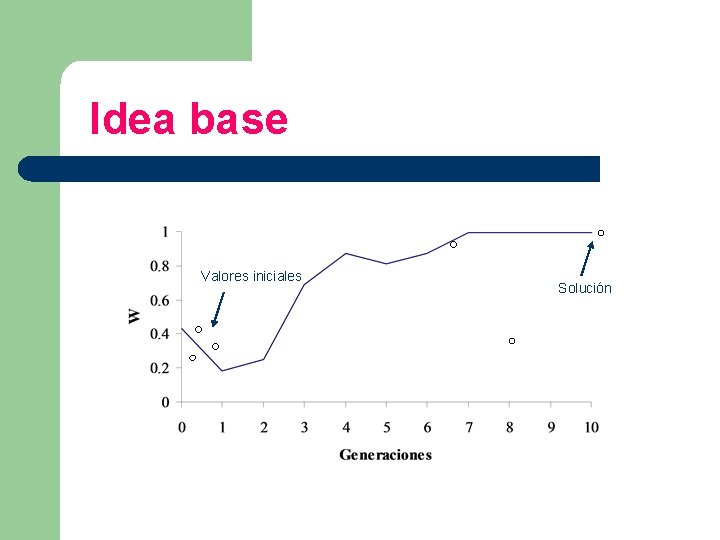
Idea base Valores iniciales Solución

Resumiendo ¡En un algoritmo genético el entorno es el problema a resolver y los organismos las posibles soluciones del mismo!

Resumiendo Para poder aplicar un AG a un problema debemos determinar: a) Una codificación genética para el problema. b) Una función de ajuste (eficacia o fitness) que asigne un valor a cada individuo de acuerdo con su

Resumiendo Los AG’s tradicionales manejan cadenas de símbolos de longitud fija llamadas cromosomas. Asociado a cada una de las posiciones de la cadena hay un gen. Los símbolos que constituyen un gen se llaman alelos (0/1 en el caso

¿Cómo se realizan? 1. - Trabajamos con poblaciones de posibles soluciones a nuestro problema. Para que haya “evolución” tiene que haber variación sobre la que pueda actuar la “selección natural”.

¿Cómo se realizan? 2. - Cada posible solución depende de un conjunto de parámetros que tomarán unos valores u otros. parámetros 0 0 1 0 0 0 = individuo (cromosoma) de una población
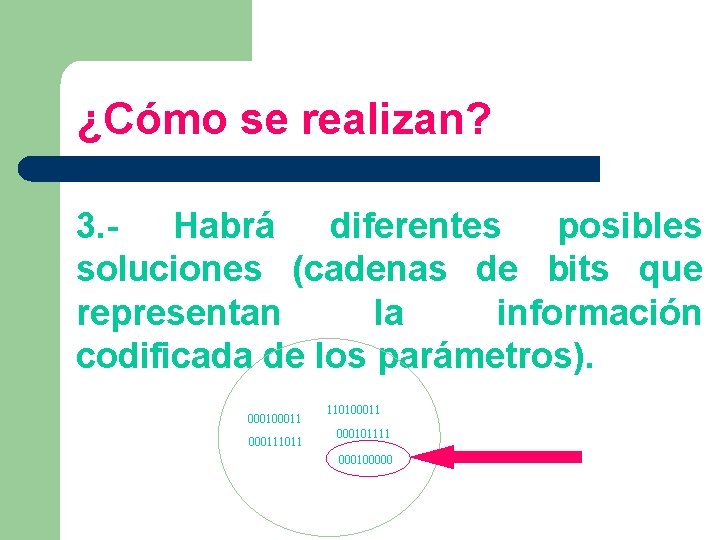
¿Cómo se realizan? 3. Habrá diferentes posibles soluciones (cadenas de bits que representan la información codificada de los parámetros). 000111011 110100011 000101111 000100000

¿Cómo se realizan? 4. - Debemos asociar una función de idoneidad o “fitness” a cada una de estas posibles soluciones. ¿sobrevive? “Fitness” = 0. 0 Solución x

¿Cómo se realizan? 4. - Debemos asociar una función de idoneidad o “fitness” a cada una de estas posibles soluciones. “Fitness” = 0. 0 No sobrevive

Algoritmo Genético Simple (SG ESTRUCTURA DEL SGA 1. - Generar al azar N “individuos”. 2. - Calcular la eficacia de cada individuo de la población. 3. - Elegir 2 progenitores de modo que la probabilidad de ser elegido (dejar hijos) sea directamente proporcional a la eficacia (“fitness proportionate selection”). 4. - De cada par de padres obtener 2 hijos mediante recombinación. 5. - Repetir el paso 3 hasta alcanzar el tamaño poblacional N. 6. - La nueva población sustituye a la antigua.

Características del SGA 1. - En cada generación los individuos dejan descendencia en función del valor medio de la población. 2. - El tamaño poblacional N permanece constante.

Características del SGA Para usar algoritmos genéticos debemos codificar las distintas soluciones de modo que sea posible hacer que evolucionen (recombinen y muten).

Ejercicio 1 Poner en pseudocódigo (independiente del lenguaje de programación) el SGA para un problema de 8 bits (longitud del cromosoma)

Ejercicio 1 0. - Declarar e inicializar variables…

Ejercicio 1 1. - Generar al azar N individuos (N << 28) Para i= 1 hasta N individuo[i]=parte entera de[uniform()× 28]

Ejercicio 1 2. - Calcular la eficacia de cada individuo de la población y la media poblacional Para i= 1 hasta N eficacia[i] = Obten. Eficacia(individuo[i]) sum. Eficacia += eficacia[i]

Ejercicio 1 3, 4 y 5. - Elegir padres y obtener N hijos Repetir hasta obtener N hijos padre 1 = Obten. Padre() padre 2 = Obten. Padre() //obtener 2 hijos mediante recombinación:

Ejercicio 1 6. - La nueva población sustituye a la vieja Para i= 1 hasta N individuo[i] = hijo[i]

Ejercicio 1 7. - Mutar y volver al paso 2 hasta terminar las generaciones o alcanzar un valor especificado (p. ej. eficacia promedio = 1) muta(poblacion) // poblacion es un vector de N individuos

Métodos de representación 1. - Binaria: Cada alelo de un cromosoma consta de 0/1. 2. - Real: Cada alelo es un nº real. 3. - Longitud fija: Cromosomas de n bits 4. - Longitud variable: Reales o binarios

Métodos de selección 1. - Selección proporcional (a la eficacia): A mayor eficacia probabilidad de más hijos (no es determinista). 2. - Selección por torneo: Se seleccionan q soluciones y gana la mejor. Se repite el proceso hasta generar N nuevos hijos. 3. - Selección por rango: Se ordenan las soluciones según su valor de fitness. 4. - Estrategia evolutiva ( + )ES: Se seleccionan determinísticamente soluciones de un total de paternas + hijos.

Métodos de recombinación Existen distintos métodos para realizar la recombinación: 1. - Entrecruzamiento de 1 punto: Sólo un punto de cruce. 2. - Entrecruzamiento de n puntos: Se usa bastante con n = 2 3. - Entrecruzamiento uniforme: El nº de puntos no está fijado. La decisión de insertar un punto de ruptura es independiente para cada bit del cromosoma.

Cálculo de la eficacia de un indi • Para cada individuo i se calcula el valor de la función de idoneidad o función objetivo (la queremos maximizar) f(i) • Sea fprom(t) la media de las funciones de idoneidad de la población en la generación t • La fitness del individuo i será w(i) = f(i) / fprom(t)

¿Por qué funcionan los AGs? l Esquema: Subconjunto de cadenas con similitudes en ciertas posiciones (1 # # 0). l Orden de un esquema: El nº de alelos definidos en él. l Longitud de un esquema: La distancia entre el primero y último de

¿Por qué funcionan los AGs? l Teorema Fundamental de los AGs (de los esquemas): Esquemas cortos, de orden bajo y con eficacia por encima de la media, incrementan el nº de representantes en las generaciones sucesivas de un AG.

Problemas de los AGs l Decepción: Algunos esquemas cortos y de bajo orden pueden engañar al algoritmo y hacerle converger en soluciones subóptimas.

Problemas de los AGs l Función decepcionante: Cuando existen esquemas cortos de bajo orden y alta eficacia que no proporcionan la solución óptima.

Problemas de los AGs l Epistasis: No independencia en el efecto de los distintos genes (bits) sobre el valor de eficacia del individuo. Existen diferentes modos de medir la epistasis de una codificación (ej: varianza de la epistasis, Davidor 1991).

Ejercicio 2 Escribir en C o en otro lenguaje de programación una función que cuente el nº de 1’s en una cadena de 8 bits

Código : Valor del individuo double d_obten. Unos(int cromosoma, int nbits) {/* Devuelve un valor mayor cuantos más 1’s tenga el cromosoma */ /*variables*/ int pos, sum. Unos=0, control=1; for(pos=0; pos< nbits; pos++){ // para todas las posiciones // identifica si hay un 1 en la posición pos y lo cuenta if(control&cromosoma) sum. Unos++; control =control<< 1; // sucesivas potencias de 2 } return ((double)sum. Unos); }

ALGORITMOS GENÉTICOS Día 2

Ejercicio 3 Escribir en C una subrutina que realice la recombinación uniforme y libre (misma probabilidad en todas las posiciones) entre 2 cadenas de n bits

Código: Recombinación void v_Rec(int padre 1, int padre 2, int *hijo 1, int *hijo 2, int nbits) { /* Entrecruzmiento Uniforme: Recombinación libre (pr = 0. 5) entre padre 1 y 2 para producir hijos 1 y 2 */ long int EE, FF, maxval= (1<<nbits)-1; EE = i_getbin(nbits); // obtiene un nº al azar entre 0 y 2 nbits FF = ~EE; // obtiene los bits complementarios de EE FF = FF&maxval; // pone a 0 todos los bits a la izq

Ejercicio 4 Escribir en C una rutina que, dada una tasa de mutación por individuo y locus, genere los mutantes de la población.

Código: Mutación void muta(int *indiv, int N, int nbits, double mu) {/* Genera el nº de mutantes de la población para una tasa de mutación mu dada */ /*variables*/ int Num. Mut, mutante, locus=1; double tasa; tasa=(double)N*(double)nbits*mu; Num. Mut =poison(tasa); // opcionalmente: Num. Mut = (int)tasa if(Num. Mut){ // si hay al menos un mutante… for(mut=0; mut<Num. Mut; mut++){ mutante=(int)(N*uniform()); //elige 1 individuo posicion=(int)(nbits*uniform()); //elige 1 locus /* ponemos un 1 en la posición : */ locus=1<<posicion /* con el OR exclusivo ^ mutamos */ indiv[mutante]=indiv[mutante]^locus; }

SELECCIÓN La ruleta de la selección “roulette wheel selection”: Las ranuras de la ruleta tendrán un tamaño porporcional a la eficacia de cada individuo.

SELECCIÓN 0 T w 8 w 1 w 7 w 2 w 6 w 5 w 4 w 3 w 1 T = wi

SELECCIÓN • Elegir un nº j al azar entre 0 y T
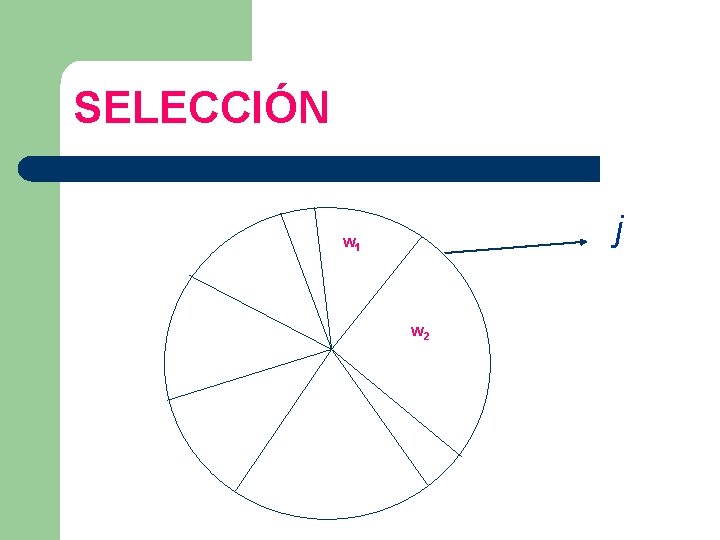
SELECCIÓN j w 1 w 2

SELECCIÓN • Recorremos los valores de fitness wi de cada individuo desde 0 hasta N

SELECCIÓN • Si la probabilidad acumulada de wi es mayor que j elegimos a i como padre sino pasamos a i+1

SELECCIÓN j w 1 w 2 w 1 + w 2

Ejercicio 5 Escribir en C una rutina que, obtenga hijos en proporción a la fitness de los padres (selección porporcional).

ALGORITMOS GENÉTICOS Día 3

Código: Selección proporcional // Código para elegir un padre (recordar que un padre es un nº entero): j=(int)(c. T*uniform()); // c. T es la suma de todas las fitness for(c. Sum=0. 0, ci=0; ci<Nini; ci++){ c. Sum+=Cw[ci]; // seleccionar el individuo cuyo valor incrementa la suma más allá del límite j: if(c. Sum>=j){ padre=individuo[ci]; break; // salimos del bucle for } }

Problema 1 Obtener, a partir de 4 cadenas obtenidas al azar, la cadena de 8 bits con mayor nº de unos (función objetivo)

Problema 1 Pistas: 1. - Generar al azar una pob de 4 individuos (4 números enteros) 2. - Calcular la fitness de cada uno y la fitness total de la población 3. - Elegir 2 padres usando el método de selección proporcional 4. - Obtener 2 hijos mediante recombinación (libre) 5. - Volver al punto 3 hasta alcanzar el tamaño de población N 6. - La nueva población sustituye a la antigua

ALGORITMOS GENÉTICOS Día 4

Sistemas de numeración Paso de binario a decimal: b 2 b 1 b 0, b-1 = (22 × b 2)+ (21 × b 1)+ (20 × b 0)+ (2 -1 × b-1) Ej: Pasar a decimal el nº binario

Sistemas de numeración Paso de decimal a binario: Para obtener la parte entera dividimos entre 2 sucesivamente hasta que el resultado sea 1 o 0. El nº binario buscado es el último resultado obtenido seguido de todos los restos de las sucesivas divisiones.

Sistemas de numeración Paso de decimal a binario: Para obtener la parte decimal multiplicamos por 2 sucesivamente, si el resultado es menor que 1 ponemos un 0 sino ponemos un 1. En este último caso restamos 1 y continuamos. El nº binario buscado es la ristra de 0’s

Codificar reales con enteros binarios Pasos para obtener desde un nº binario un nº real con una precisión y rango dados: 1. - Pasar la cadena binaria a un nº en base 10 2. - Hallar el nº real correspondiente al dominio [-1. . 2] y con la precisión
![Codificar reales con enteros bin ¿Cuántos bits necesitamos? Longitud del dominio [-1. . 2] Codificar reales con enteros bin ¿Cuántos bits necesitamos? Longitud del dominio [-1. . 2]](http://slidetodoc.com/presentation_image_h/91da18dd1490bf73305739842d28925f/image-61.jpg)
Codificar reales con enteros bin ¿Cuántos bits necesitamos? Longitud del dominio [-1. . 2] = 3. Para obtener una precisión de 6 dígitos debemos dividir el rango en 3 × 106 rangos de igual tamaño. 221 < 3 × 106 < 222 nbits = ceil(log 2(rango × 10 precision)) =22

Codificar reales con enteros bin Sea la cadena bn…b 2 b 1 b 0 1) Obtenemos el entero positivo x’ en base 10 2) Obtenemos el real x en el dom [1. . 2] tal que x = inf + x’ long / (2 nbits -1 ) = -1 + x’ 3 /

Problema 2 Dada la función f(x) = xsen(10 x) + 1. 0 encontrar el valor de x perteneciente a [-1. . 2] que maximice la función. Se pide una precisión de 6 decimales tras el punto.

Problema 2 El valor f(x) será el valor de eficacia. A mayor f(x) mayor nº de hijos dejará un individuo x. La mutación y recombinación son las ya vistas para una cadena de bits.

Problema 2 Escribir la función que obtiene la fitness para este problema: La función de obtención de la fitness será simplemente la función que pase una cadena binaria al correspondiente nº real x y calcule f(x).

Problema 2 Lo que resta es muy similar a lo hecho para el problema 1.

Problema 2 Pistas: 1. - Generar al azar una pob de 4 individuos (4 números enteros) 2. - Calcular la fitness de cada uno y la fitness total de la población 3. - Elegir 2 padres usando el método de selección proporcional 4. - Obtener 2 hijos mediante recombinación (libre) 5. - Volver a 3 hasta alcanzar el tamaño de población N 6. - La nueva población sustituye a la antigua 7. - Mutar y volver a 2 hasta alcanzar Max generaciones o

ALGORITMOS GENÉTICOS Día 5

APLICACIONES EN BIOLOGÍA Diseño de cebadores usando algoritmos genéticos.

APLICACIONES EN BIOLOGÍA El diseño de primers es una tarea tediosa en la que hay que tener en cuenta diversas restricciones

APLICACIONES EN BIOLOGÍA Reglas generales para el diseño de primers

APLICACIONES EN BIOLOGÍA PARÁMETROS A CONSIDERAR Tamaño del oligonucleótido: 20 -25 nt Temperatura de fusión (Tm): Tm = 2(A+T) + 4(G+C) Fórmula de Wallace. Tm = 59. 9 + 0. 41 (%G+C) – 675/tamaño Especificidad: En general, una temperatura de fusión de 55°C – 72°C es la más adecuada (Corresponde a un tamaño de oligonucleótido de 18– 24 bases según la

Bibliografía l Davidor, Y. 1991. Epistasis variance: a viewpoint on GAhardness. In Rawlins, G. (ed. ), Foundations on Genetics Algorithms, Morgan Kauffman, Berlin, 23 -25. l Michalewicz, Z. 1996. Genetic Algorithms + Data Structures = Evolution Programs, Springer Verlag. l Mitchell, M. 1996. An Introduction to Genetic Algorithms, MIT Press, Massachusetts. l Whitley, D. 2000. An overview of evolutionary algorithms: practical issues and common pitfalls.
- Slides: 73