Gnopole Institut Pasteur Bioinformatique Bilan 2003 Ivan Moszer

Génopole Institut Pasteur Bioinformatique - Bilan 2003 Ivan Moszer Génopole Institut Pasteur Plate-forme “Intégration et Analyse Génomiques” Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Activités et missions â Annotation de nouvelles séquences génomiques : développement d’outils d’annotation et de stratégies adaptées ; formation aux unités de recherche â Maintien de collections de données génomiques, identifiables par des annotations de grande qualité, sur un ensemble d'organismes sélectionnés : collaborations avec les unités compétentes, rôle de formation et de standardisation â Développement logiciel de bases de données génomiques innovantes (structures de données, interfaces utilisateur) : génome (projet Geno. List), transcriptome, et protéome (=> système intégré) â Développement et application de méthodes d'analyse mathématiques et statistiques pour le décryptage des données génomiques : génomique comparée, études phylogénétiques, analyse des données d'expression, réseaux de régulation, etc. â Enseignement et formation Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 2

Ligne directrice des activités 3 Le pourquoi et le comment des bases de données génomiques â 1. Concevoir et implémenter des structures de données ad hoc â 2. S’assurer que celles-ci sont alimentées par des données de grande qualité â 3. Concevoir et implémenter des interfaces utilisateur ad hoc ß Ces bases de données agissent comme un point de rencontre entre données de qualité organisées selon des schémas adéquats, et outils d’interrogation et d’analyse pertinents, accessibles depuis des interfaces utilisateur conçues en premier lieu pour répondre aux besoins des biologistes ß L’accès à de tels environnements logiciels intégrés doit aider à la découverte de connaissances, au travers d’une exploration des données facilitée par des interactions homme-machine inspirées par les utilisateurs spécialistes, et des représentations visuelles judicieusement élaborées Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Outils d’annotation (L. Frangeul et al. ) â Programme « CAAT-Box » : « Contig Assembly and Annotation Tool-Box » â Caractéristiques : – – – Suivi du shotgun et des assemblages successifs Méthodes pour la finition Annotation possible dès l’étape de finition Annotations accessibles et modifiables via le Web Modules d’annotation (Blast, Gene. Mark, frameshifts, « primers » , etc. ) â Applications : – – – Annotation des génomes de Listeria monocytogenes et Listeria innocua Annotation du génome de Photorhabdus luminescens Annotation du génome de Streptococcus agalactiae Annotation du génome de Candida albicans Annotation du génome de Candida glabrata â Participation au projet Geno* Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 4

CAAT-Box Motivations â Pourquoi commencer à annoter un génome non terminé ? – – Nombreuses séquences obtenues en peu de temps Ces séquences sont souvent assemblées automatiquement, générant de grands contigs â Quelles sont les difficultés ? – – Changement des séquences et des contigs après chaque assemblage D’où une modification de la localisation/nomenclature/séquence des gènes déjà annotés Annotation Finishing Shotgun 2002 1996 Time needed Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 5
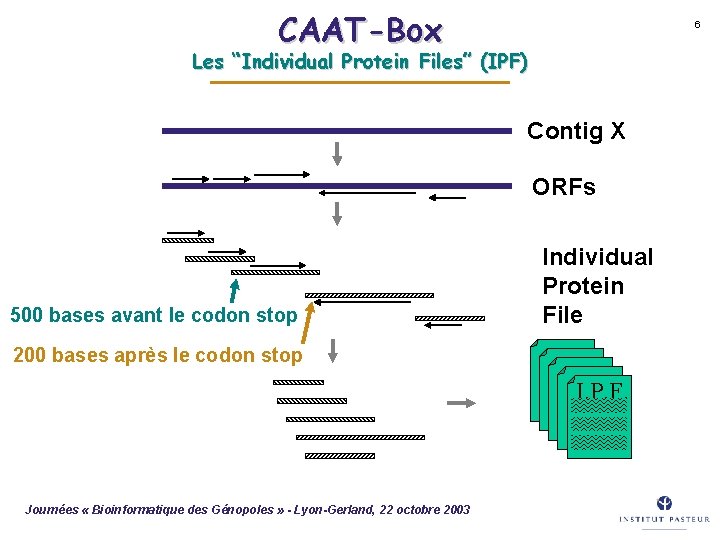
CAAT-Box 6 Les “Individual Protein Files” (IPF) Contig X ORFs 500 bases avant le codon stop Individual Protein File 200 bases après le codon stop I. P. F. Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
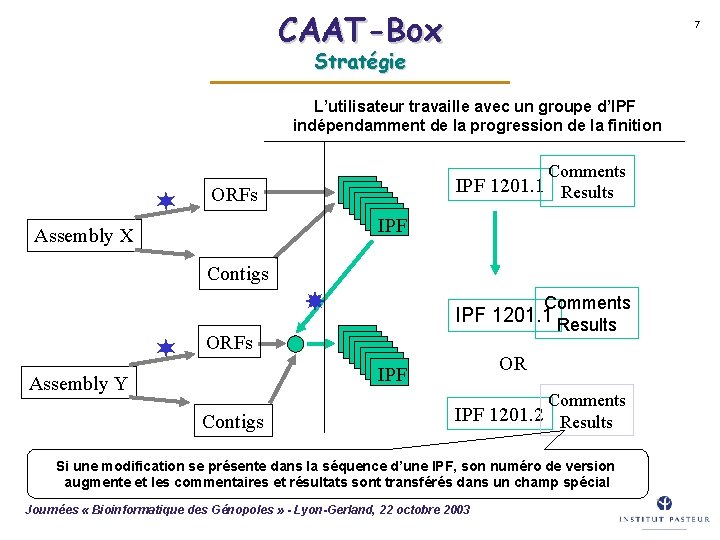
CAAT-Box 7 Stratégie L’utilisateur travaille avec un groupe d’IPF indépendamment de la progression de la finition Comments ¬ IPF 1201. 1 Results ORFs IPF Assembly X Contigs ¬ Comments IPF 1201. 1 Results ORFs OR IPF Assembly Y Contigs Comments IPF 1201. 2 Results Si une modification se présente dans la séquence d’une IPF, son numéro de version augmente et les commentaires et résultats sont transférés dans un champ spécial Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
Interface de CAAT-Box Utilitaires Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 8

Interface de CAAT-Box 9 Page IPF_reader. cgi génère dynamiquement une page html en fonction : • des champs du fichier IPF • du niveau d’accès utilisateur • des fichiers IPF_results pour cette IPF • des commentaires utilisateur sur cette IPF Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
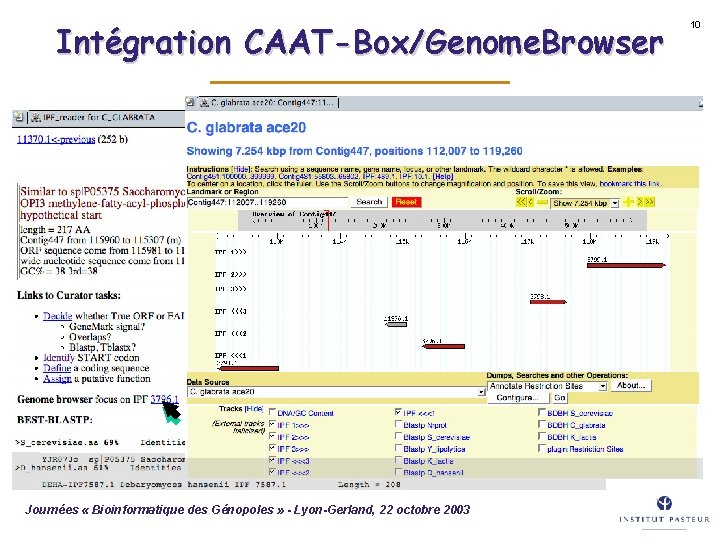
Intégration CAAT-Box/Genome. Browser Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 10

Bases de données annotées 11 (C. Boursaux-Eude et al. ) â Objectif : générer des annotations de grande qualité pour les génomes microbiens – – Relier séquence et fonctions cellulaires Exigences de qualité et de cohérence : • • – – Contrôle, correction, et validation des annotations existantes Création de nouvelles annotations (physiques et fonctionnelles) Vérification expérimentale des prédictions in silico (interprétations trop permissives, danger des seuils automatiques, manque d’attributs « warning » , manque de traçabilité, propagation des erreurs) Nomenclatures et vocabulaires contrôlés Références croisées Mises à jour régulières â Applications : – – Mise à jour du génome de Bacillus subtilis (mai 2001) (coll. A. Danchin) Mise à jour des génomes de Mycobacterium tuberculosis et Mycobacterium leprae (janvier 2002) (coll. S. T. Cole) Mise à jour des génomes de Helicobacter pylori 26695 et J 99 (coll. A. Labigne) Projets pour plusieurs autres organismes microbiens (dont Staphylococcus aureus, Saccharomyces cerevisiae, etc. ) â Participation au projet HAMAP (SWISS-PROT) Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Subti. List update (May 2001) â 288 sequence corrections (systematic verifications and individual submissions) â 520 references imported and linked to the relevant genes â Updated genes Nb of genes – Genomic sequence changed • • – • • “y” not-“y” “y” Description updated 67 18 ( 9) 3 ( 1) 5 2 85 location updated (start and/or stop codons) new genes added in the annotations genes deleted from the annotations Gene name changed • – location updated (start and/or stop codons) substitutions 3 internal compensated frameshift 2 two genes merged into one single gene three genes merged into one single gene one gene split out into two genes 3 ( 6) new genes added in the annotations genes deleted from the annotations Genomic sequence unchanged • 103 71 8 6 239 181 54 4 ~800 Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 12
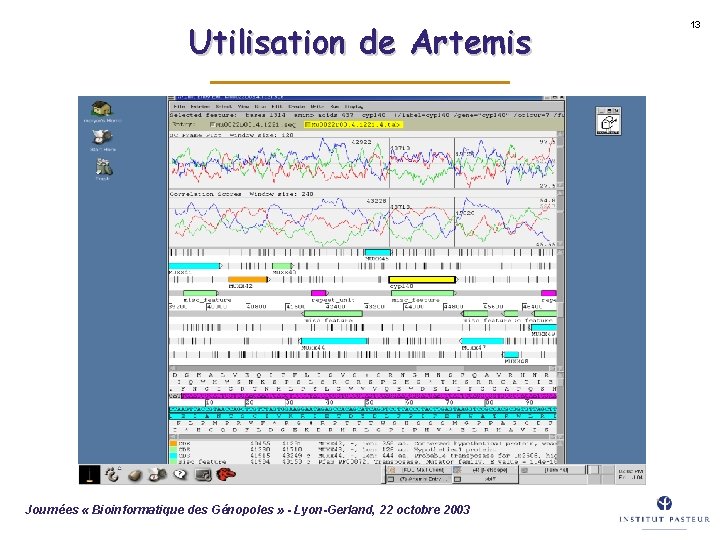
Utilisation de Artemis Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 13

Tubercu. List updates â Tubercu. List R 4 (July 2002) – – – – 82 new CDS 60 CDS lengths modified 400 new gene names Mycobacterial ortholog table (links to Leproma) Transcriptomic section (techniques and conditions) Proteomic section (links to databases) Current list of Mycobacterial Intergenic Repetive Units (MIRU) 1, 000 targeted citations – most with medline links â Tubercu. List R 5 (April 2003) – – – 10 CDS lengths modified ~ 50 new gene names 1, 000 targeted citations – all with medline links (citations added directly to Tubercu. List using Biblio. DB) Updated transmembrane analysis (TMHMM) More detailed functional classification Updated partition analysis (MEME/MAST) of the proteome Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 14
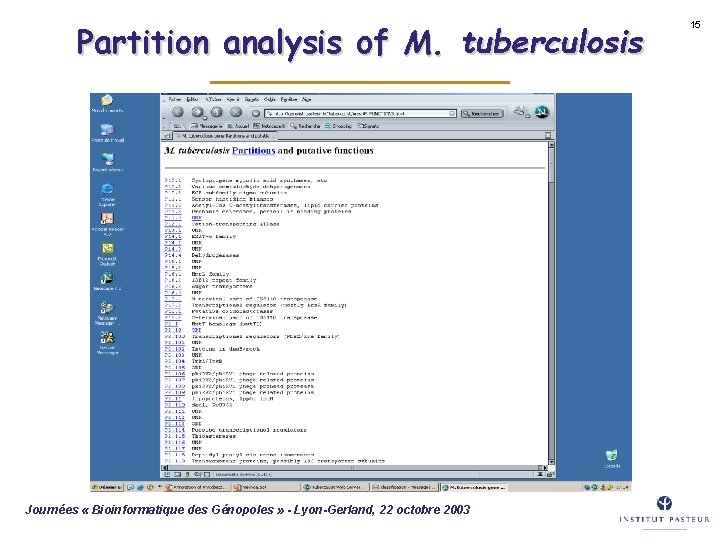
Partition analysis of M. tuberculosis Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 15

Bases de données génomiques 16 (S. Moreira et al. ) â Conception d’un modèle de données générique « Geno. List » et implémentation d’une interface pour le biologiste â Application de Geno. List à plusieurs génomes bactériens : – B. subtilis, E. coli, M. tuberculosis/leprae, H. pylori, Mycoplasma pulmonis, Synechocystis/Anabaena, L. monocytogenes/innocua, S. aureus, etc. â Extension du modèle aux relations multi-organismes (gènes orthologues, opérons conservés, signaux communs, etc. ), et de l’interface aux outils de génomique comparée (analyse de souches multiples et d’organismes proches) â Développement d’extensions pour génomes eucaryotes (C. albicans, S. cerevisiae, participation au projet Anopheles gambiae) â Réécriture en Java (utilisation du serveur applicatif Web. Objects) Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
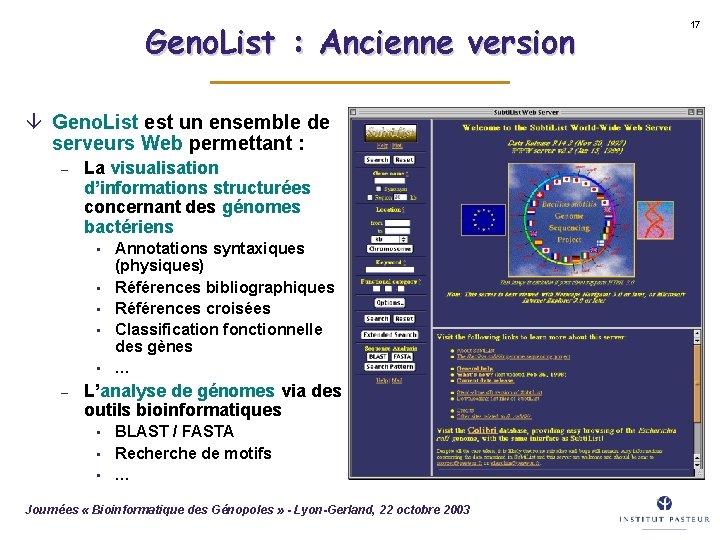
Geno. List : Ancienne version â Geno. List est un ensemble de serveurs Web permettant : – La visualisation d’informations structurées concernant des génomes bactériens • • • – Annotations syntaxiques (physiques) Références bibliographiques Références croisées Classification fonctionnelle des gènes … L’analyse de génomes via des outils bioinformatiques • • • BLAST / FASTA Recherche de motifs … Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 17

Bases de données “Geno. List” actuelles 18 http: //genolist. pasteur. fr/ â Bacillus subtilis 168: Subti. List (coll. A. Danchin - IP) â Escherichia coli K 12: Colibri (coll. K. Rudd - Miami U. ) â Mycobacterium tuberculosis H 37 Rv: Tubercu. List (coll. S. Cole - IP) â Helicobacter pylori 26695/J 99: Pylori. Gene (coll. A. Labigne - IP, P. Legrain - Hybrigenics) â Mycoplasma pulmonis UAB CTIP: Mypu. List (coll. A. Blanchard, I. Chambaud - IP) â Mycobacterium leprae TN: Leproma (coll. S. Cole - IP) â Synechocystis PCC 6803/Anabaena PCC 7120: Cyano. List (coll. N. Tandeau de Marsac - IP) â Listeria monocytogenes EGD-e/Listeria innocua CLIP 11262: Listi. List (coll. P. Glaser, F. Kunst - IP) â Staphylococcus aureus N 315/Mu 50: Aureo. List (C. Boursaux-Eude - IP) â Streptococcus pneumoniae R 6/Tigr 4: Strepto. Pneumo. List (C. Boursaux-Eude - IP) â Candida albicans SC 5314: Candida. DB (coll. C. d’Enfert - IP) â Streptococcus agalactiae NEM 316: Saga. List (coll. P. Glaser, F. Kunst - IP) Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Geno. List : une base de données « multi-génomes » microbiens 19 â Extension du modèle « Subti. List » à d’autres génomes bacteriens ou microbiens base de données et serveur Web « multi-génomes » â Améliorer le niveau de généricité du modèle de données â Définir une nomenclature cohérente (noms de gènes/id) et utiliser des vocabulaires contrôlés â Améliorer les annotations de base et intégrer des données expérimentales â Tenir compte des spécificités de chaque organisme â Établir des relations évoluées entre les génomes (gènes orthologues, opérons conservés, signaux communs, etc. ) â Intégration d’outils pour les analyses différentielles de génomes â Créer des outils spécifiques pour la gestion et l’analyse des souches multiples et des organismes proches â Intégrer ces informations avec d’autres collections de données (références croisées) â Conserver une interface puissante et conviviale Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
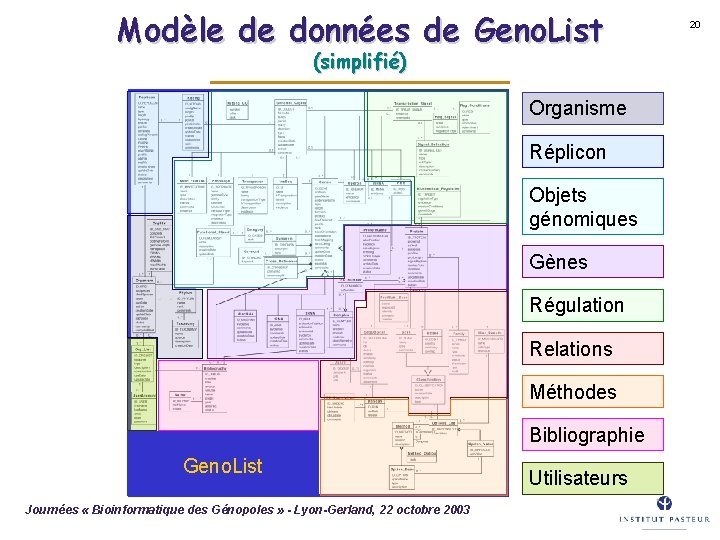
Modèle de données de Geno. List (simplifié) Organisme Réplicon Objets génomiques Gènes Régulation Relations Méthodes Bibliographie Geno. List Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 Utilisateurs 20
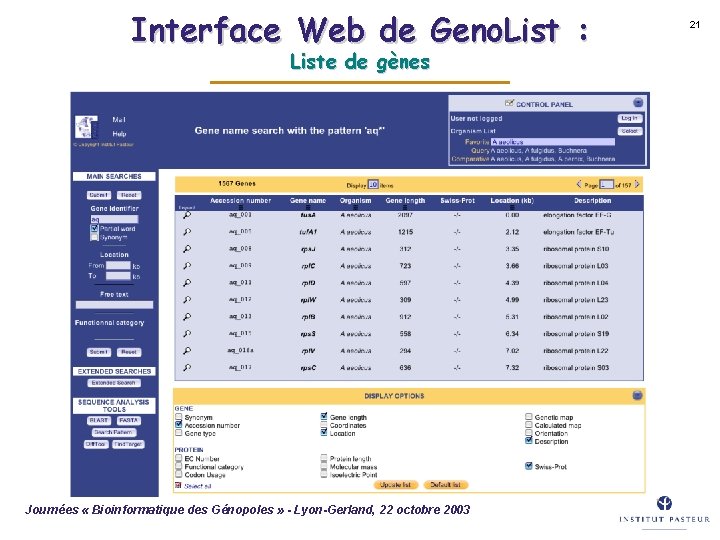
Interface Web de Geno. List : Liste de gènes Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 21
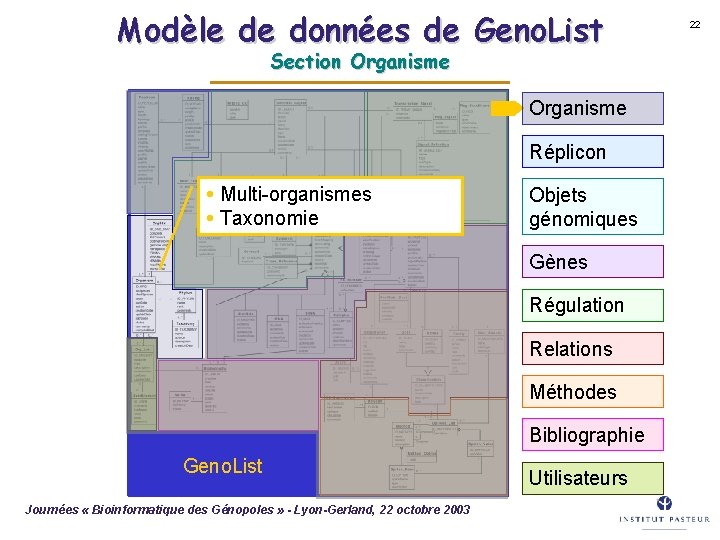
Modèle de données de Geno. List Section Organisme Réplicon Multi-organismes Taxonomie Objets génomiques Gènes Régulation Relations Méthodes Bibliographie Geno. List Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 Utilisateurs 22

Interface Web de Geno. List : Sélection taxonomique d’organismes Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 23
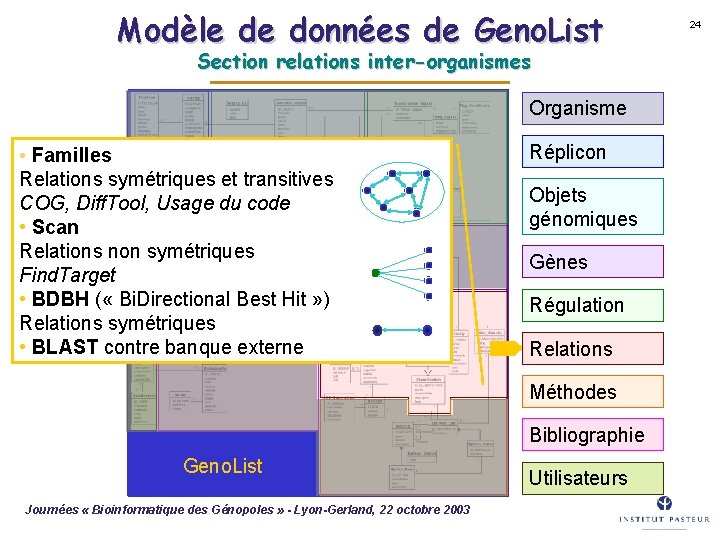
Modèle de données de Geno. List Section relations inter-organismes Organisme • Familles Relations symétriques et transitives COG, Diff. Tool, Usage du code • Scan Relations non symétriques Find. Target • BDBH ( « Bi. Directional Best Hit » ) Relations symétriques • BLAST contre banque externe Réplicon Objets génomiques Gènes Régulation Relations Méthodes Bibliographie Geno. List Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 Utilisateurs 24

Génération et intégration de données Diff. Tool 25 (1) Construction de fichiers de séquences protéiques propres à chaque organisme (protéomes) au format FASTA (2) Lancement du programme Diff. Tool (3) Production de deux fichiers : q. cluster (composition des familles) q. legend (description des familles) (4) « Parsing » des fichiers de sortie issus de Diff. Tool (5) Intégration des données dans la base Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
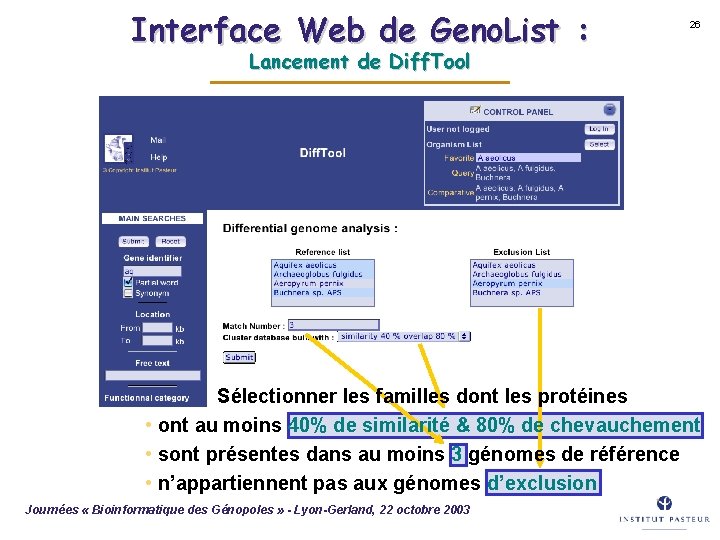
Interface Web de Geno. List : 26 Lancement de Diff. Tool Sélectionner les familles dont les protéines • ont au moins 40% de similarité & 80% de chevauchement • sont présentes dans au moins 3 génomes de référence • n’appartiennent pas aux génomes d’exclusion Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
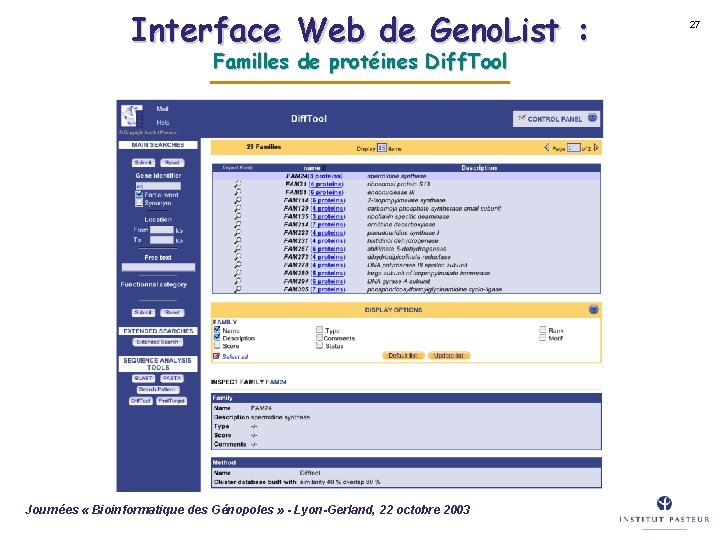
Interface Web de Geno. List : Familles de protéines Diff. Tool Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 27
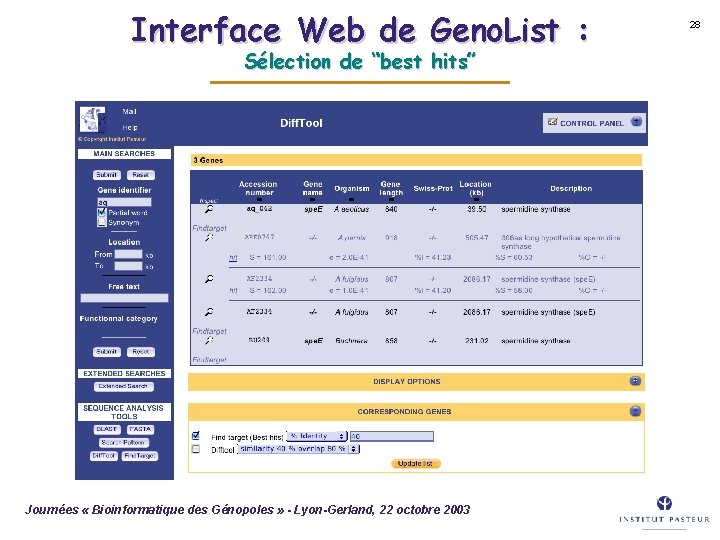
Interface Web de Geno. List : Sélection de “best hits” Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 28
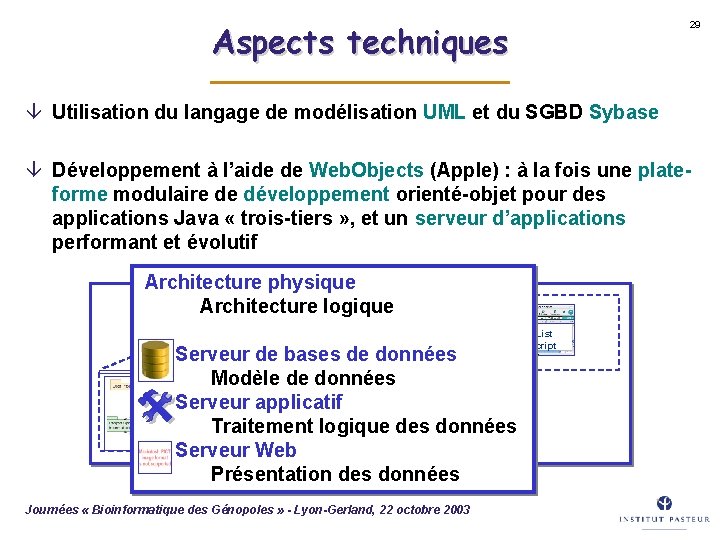
Aspects techniques 29 â Utilisation du langage de modélisation UML et du SGBD Sybase â Développement à l’aide de Web. Objects (Apple) : à la fois une plateforme modulaire de développement orienté-objet pour des applications Java « trois-tiers » , et un serveur d’applications performant et évolutif Architecture physique Architecture logique Geno. List Sub. Script Serveur de bases de données Modèle de données Serveur applicatif Traitement logique des données Serveur Web Présentation des données Sybase Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Bases de données transcriptomiques 30 (S. Moreira et al. ) â Développement dans le cadre d’un projet européen ( « BACELL Network » ) sur les réseaux de régulation chez B. subtilis â Intégration des conditions expérimentales, des résultats bruts et traités, et des analyses ultérieures â Schéma conforme aux recommandations MIAME/MGED â Intégration d’outils d’analyse statistique â Objectif générique pour une réutilisation dans un cadre plus large (P. falciparum, E. coli, S. agalactiae, etc. ) â Interface Web développée en Java (utilisation du serveur applicatif Web. Objects) Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
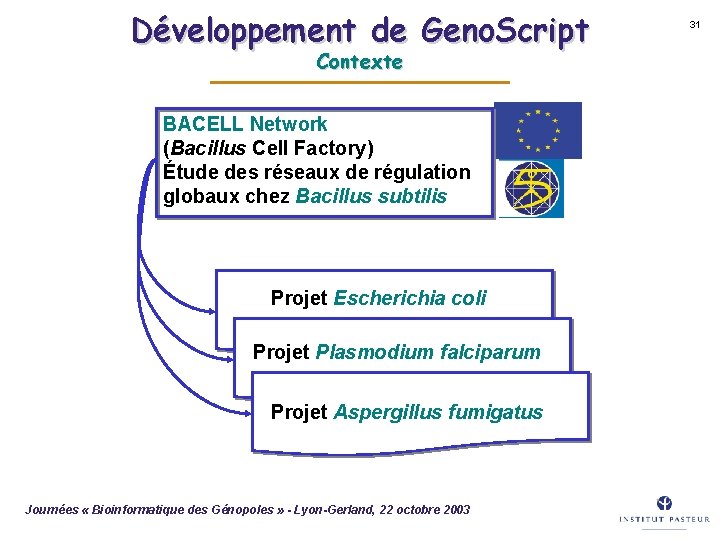
Développement de Geno. Script Contexte BACELL Network (Bacillus Cell Factory) Étude des réseaux de régulation globaux chez Bacillus subtilis Projet Escherichia coli Projet Plasmodium falciparum Projet Aspergillus fumigatus Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 31

Modèle conceptuel de données (simplifié) Overview Login, Context, Protocols Experimental Analysis Hybridisation Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 Array Design 32
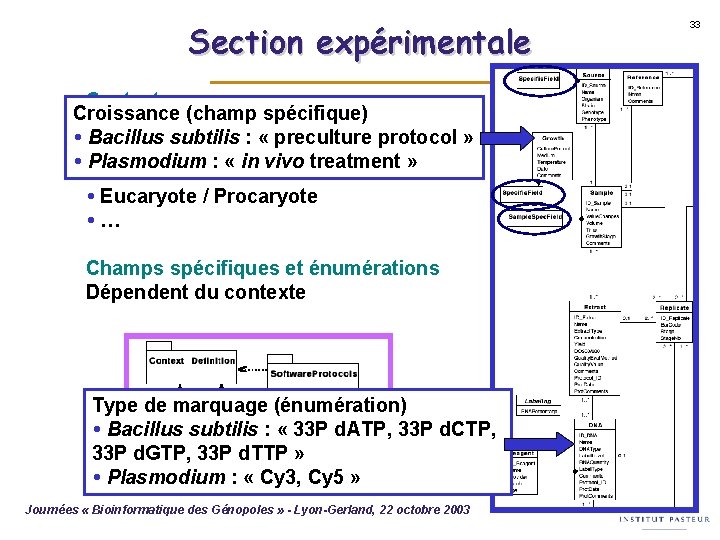
Section expérimentale Contexte Croissance (champ spécifique) Définit les conditions techniques de Bacillus subtilis : « preculture protocol » réalisation de l’expérience Plasmodium : « in vivo treatment » Lame de verre / membrane Eucaryote / Procaryote … Champs spécifiques et énumérations Dépendent du contexte Type de marquage (énumération) Bacillus subtilis : « 33 P d. ATP, 33 P d. CTP, 33 P d. GTP, 33 P d. TTP » Plasmodium : « Cy 3, Cy 5 » Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 33
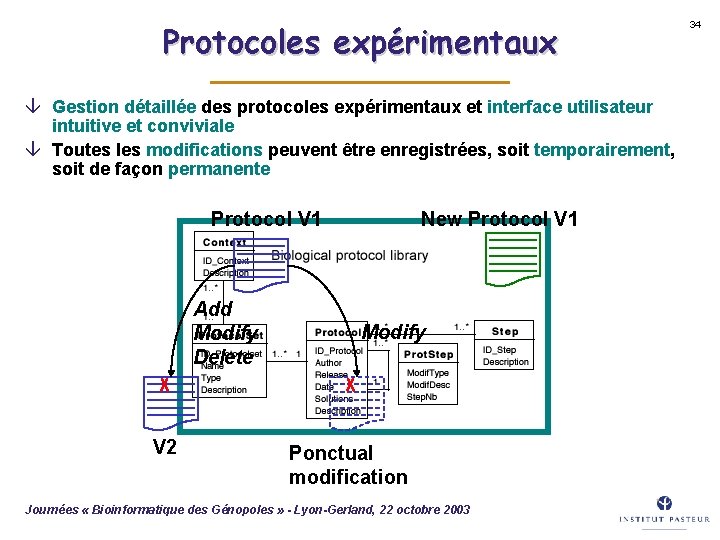
Protocoles expérimentaux â Gestion détaillée des protocoles expérimentaux et interface utilisateur intuitive et conviviale â Toutes les modifications peuvent être enregistrées, soit temporairement, soit de façon permanente Protocol V 1 Add Modify Delete V 2 New Protocol V 1 Modify Ponctual modification Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 34
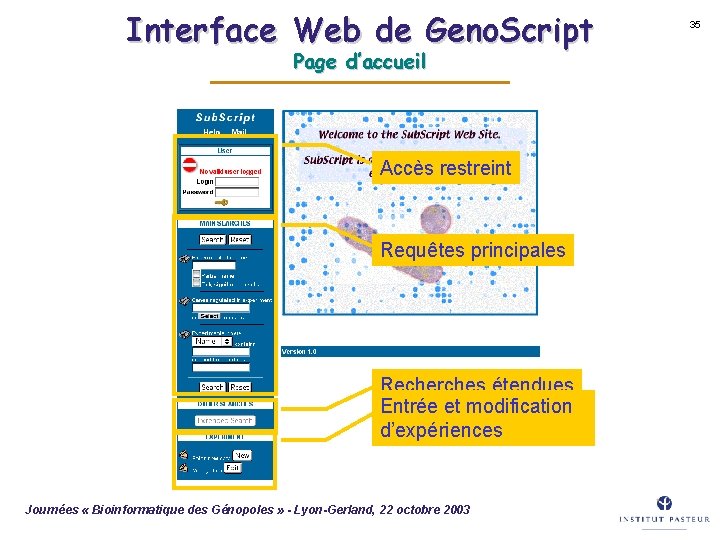
Interface Web de Geno. Script Page d’accueil Accès restreint Requêtes principales Recherches étendues Entrée et modification d’expériences Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 35
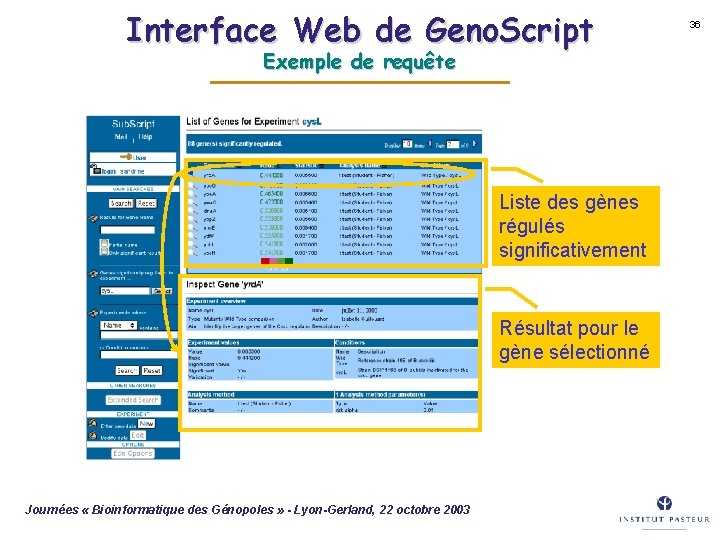
Interface Web de Geno. Script Exemple de requête Liste des gènes régulés significativement Résultat pour le gène sélectionné Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 36
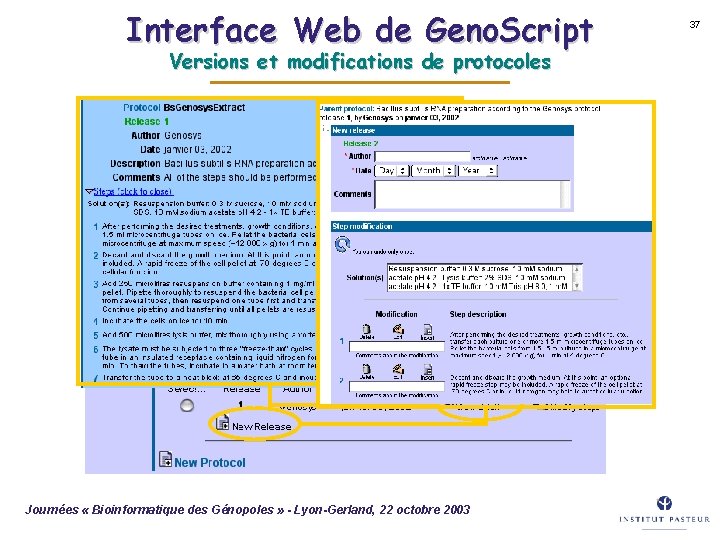
Interface Web de Geno. Script Versions et modifications de protocoles Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 37

Démarche de l’analyse statistique 38 â 1. Connaître les méthodes (principes, domaines d’application) â 2. Connaître l’expérience et les données (en termes statistiques) â 3. Connaître l’objectif (pourquoi une analyse statistique ? ) â Problèmes : Outils souvent disponibles sous la forme d’interfaces absconses (ligne de commandes), ou d’environnements très élaborés mais compliqués à utiliser ß Solution : Concevoir une plate-forme logicielle qui guide l’utilisateur au travers d’interfaces spécialisées conviviales vers les approches statistiques appropriées (outil d’aide à la décision) => interface commune et cohérente (i) à la visualisation graphique des données, (ii) aux méthodes ad hoc pour la transformation et la normalisation des données brutes, et (iii) aux tests statistiques pour l’analyse différentielle de l’expression génétique Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
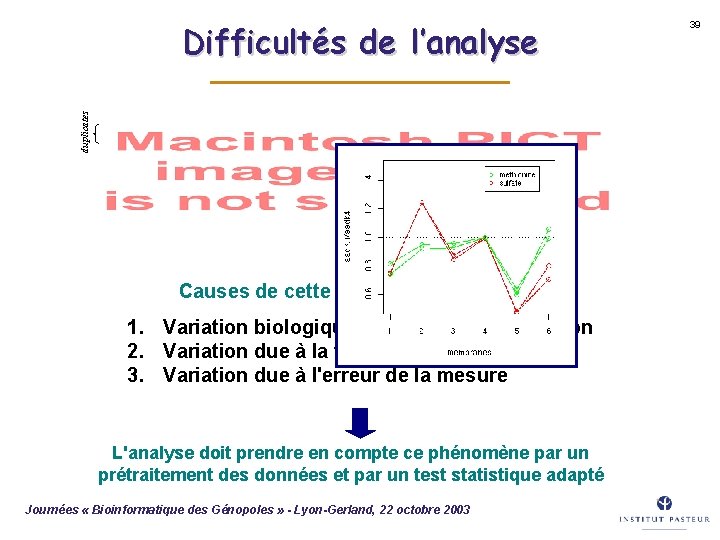
duplicates Difficultés de l’analyse Causes de cette variabilité 1. Variation biologique : intrinsèque + condition 2. Variation due à la technique 3. Variation due à l'erreur de la mesure L'analyse doit prendre en compte ce phénomène par un prétraitement des données et par un test statistique adapté Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 39

Réalisation du module statistique Objectif Prétraitement Analyse Différentielle Étapes 1. Détermination d’un protocole d’analyse 2. Implémentation des méthodes sous R + Évaluation des méthodes 3. Connecter l'environnement R à Sub. Script 4. Modification du modèle de Subscript 5. Développer l'interface de manière flexible, didactique, et documentée Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 40
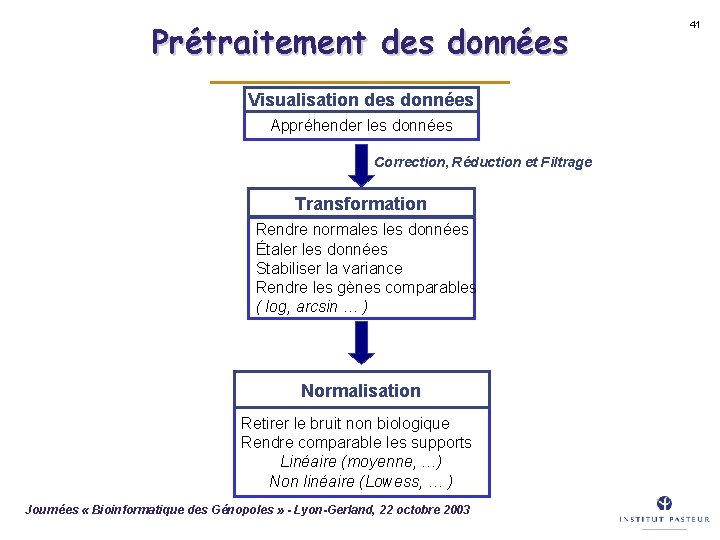
Prétraitement des données Visualisation des données Appréhender les données Correction, Réduction et Filtrage Transformation Rendre normales données Étaler les données Stabiliser la variance Rendre les gènes comparables ( log, arcsin … ) Normalisation Retirer le bruit non biologique Rendre comparable les supports Linéaire (moyenne, …) Non linéaire (Lowess, … ) Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 41
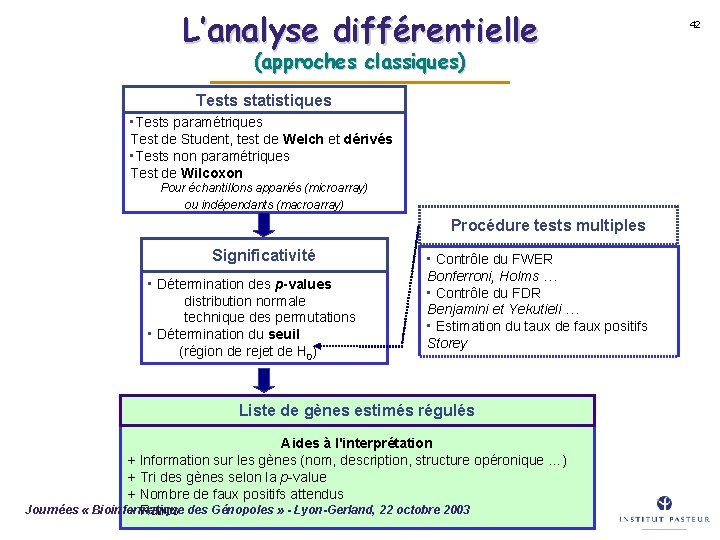
L’analyse différentielle (approches classiques) Tests statistiques • Tests paramétriques Test de Student, test de Welch et dérivés • Tests non paramétriques Test de Wilcoxon Pour échantillons appariés (microarray) ou indépendants (macroarray) Procédure tests multiples Significativité • Détermination des p-values distribution normale technique des permutations • Détermination du seuil (région de rejet de H 0) • Contrôle du FWER Bonferroni, Holms … • Contrôle du FDR Benjamini et Yekutieli … • Estimation du taux de faux positifs Storey Liste de gènes estimés régulés Aides à l'interprétation + Information sur les gènes (nom, description, structure opéronique …) + Tri des gènes selon la p-value + Nombre de faux positifs attendus Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 + Ratios 42
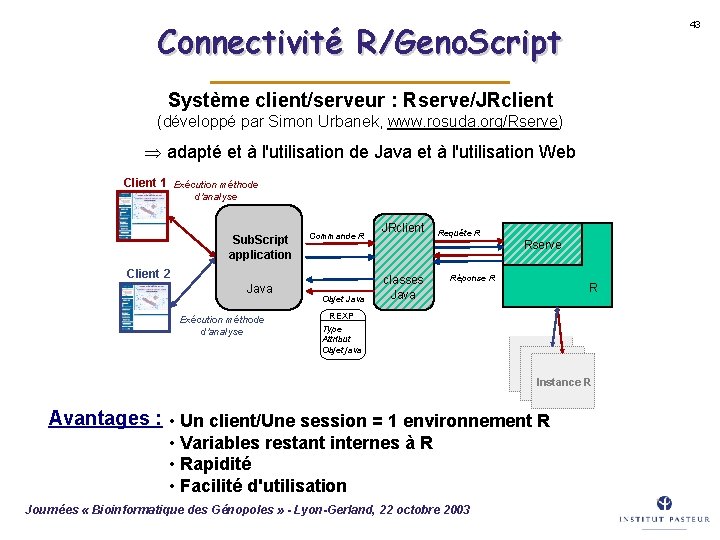
Connectivité R/Geno. Script 43 Système client/serveur : Rserve/JRclient (développé par Simon Urbanek, www. rosuda. org/Rserve) adapté et à l'utilisation de Java et à l'utilisation Web Client 1 Exécution méthode d'analyse Sub. Script application Commande R Client 2 Java Exécution méthode d'analyse Objet Java JRclient classes Java Requête R Rserve Réponse R R REXP Type Attribut Objet java Instance R Avantages : • Un client/Une session = 1 environnement R • Variables restant internes à R • Rapidité • Facilité d'utilisation Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
Interface Web de Geno. Script Prétraitement - Overview Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 44
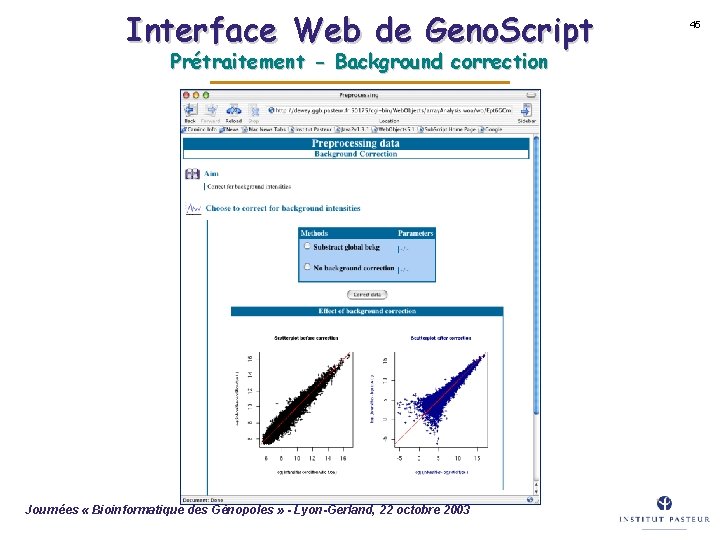
Interface Web de Geno. Script Prétraitement - Background correction Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 45
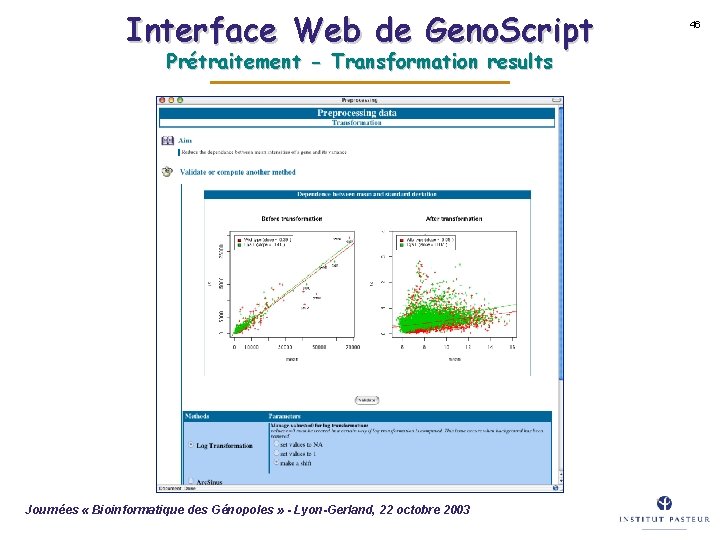
Interface Web de Geno. Script Prétraitement - Transformation results Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 46

Interface Web de Geno. Script Prétraitement - Normalisation results Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 47
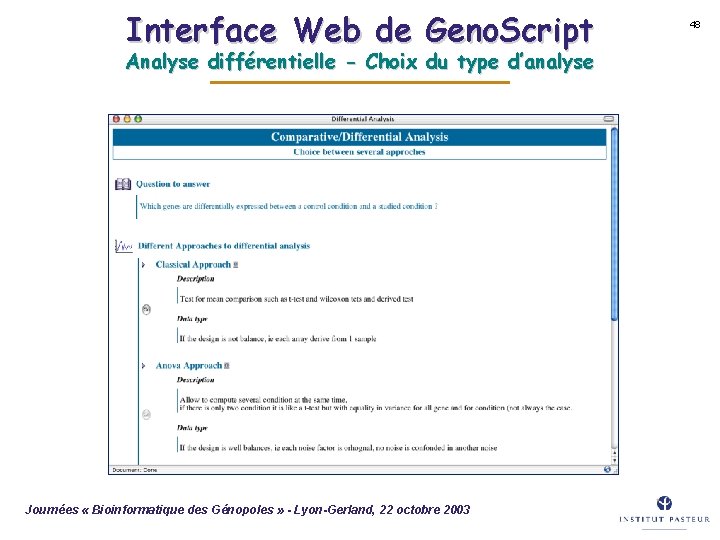
Interface Web de Geno. Script Analyse différentielle - Choix du type d’analyse Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 48
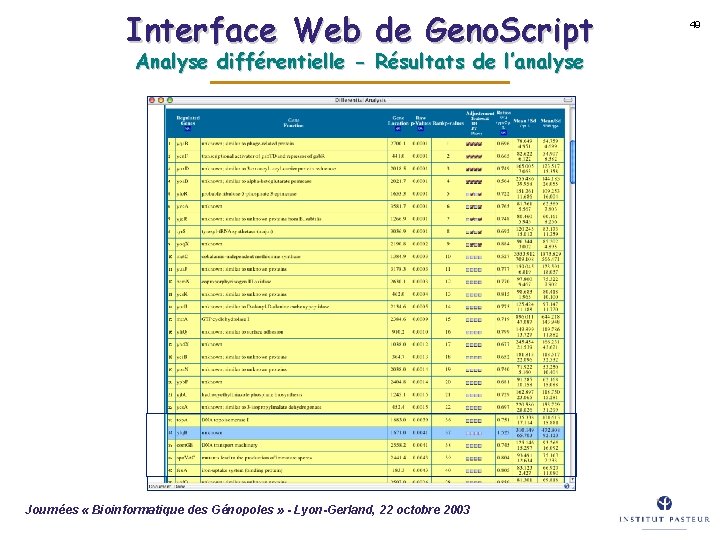
Interface Web de Geno. Script Analyse différentielle - Résultats de l’analyse Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 49

Problématique phylogénétique (C. Dauga et al. ) â Développement de méthodologies phylogénétiques mettant en évidence les transferts de gènes entre espèces proches â Étude de l’impact des différents phénomènes évolutifs que peuvent subir les gènes (transfert, recombinaison, duplication, variations de vitesse d’évolution et pression de sélection, etc. ) sur la représentation phylogénétique (arbre, valeur d’homologie) et l’évolution des génomes â Génome des procaryotes = – – – Gènes hérités verticalement + Gènes acquis par transfert + Gènes dupliqués ß Phylogénies conflictuelles : – – – pour les études de systématique pour le suivi épidémiologique de souches bactériennes pour décrire l’évolution des génomes Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 50

Identification phylogénétique des transferts â Confrontation visuelle des topologies Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 51

Évaluation des tests phylogénétiques â Quatre tests évalués : – – Incongruence (hétérogénéité des processus évolutifs ? ) Kishino-Hasegawa (topologie) Shimodaira-Hasegawa (topologie) Co-évolution (non-proportionnalité des longueurs de branche ? ) â Tests aussi performants pour détecter des transferts : – – Entre des espèces de lignées différentes Entre souches d’une même espèce Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 52

Sensibilité et spécificité â Test KH détecte 100% des gènes acquis par transferts â Test KH : pas de faux négatif â Test SH manque de sensibilité â Test SH : faux négatifs pour des transferts isolés de faible amplitude Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003 53
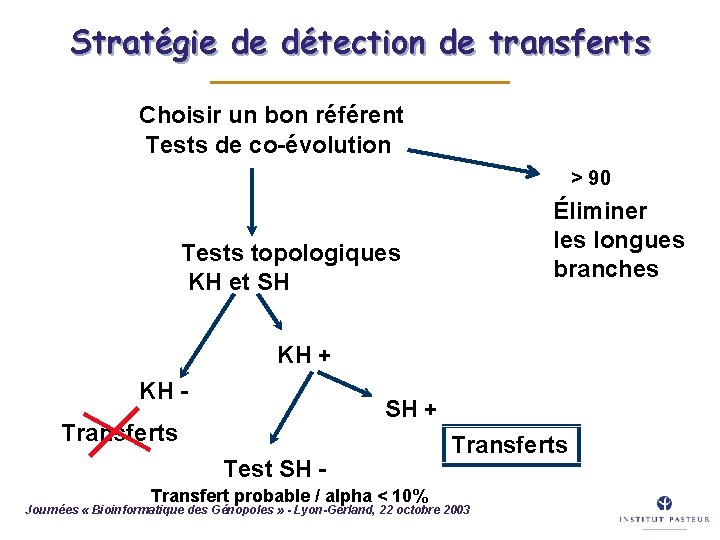
Stratégie de détection de transferts 54 Choisir un bon référent Tests de co-évolution > 90 Éliminer les longues branches Tests topologiques KH et SH KH + KH - SH + Transferts Test SH - Transfert probable / alpha < 10% Transferts Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Cours - Formations 55 â Mise en place d’une initiation à la bioinformatique pour le cours de Microbiologie Générale de l’Institut Pasteur â Participation au cours d’Analyse des Génomes de l’Institut Pasteur (traitement informatique des données) â Co-organisation de l’atelier INSERM 135 (identification de bactéries non cultivables en clinique et dans l'environnement) â Cours de formation permanente de Bioinformatique de l’Université Paris 7 â Co-organisation du cours Unesco “Microbial identification in clinical and environmental settings” â Co-organisation d’un European Training Workshop “Molecular characterization of the human intestinal microbiota” Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003

Remerciements Caroline Catherine Pierre Lionel Sandrine Nicolas Magali J. -Christophe Olivier Benjamin Sylvette Laurence Gaëlle Albane Hocine Anne Laetitia Sandrine Hafed Melinda Emmanuel David Boursaux-Eude Dauga Dehoux Frangeul Moreira Beaume Brugnon Camus Garcia Giletti Grandino Hummel Lacourrège Le Roch Madoui Marcel Marisa Mativet Nedjari Pryor Quevillon Simon 56 Louis Jones Catherine Jorge Ivo Hilde Nicole Bernard Christophe Antoine Philippe Frank Farid Jean-Yves (PI • IP) Gomperts Boneca (PBM • IP) de Reuse (PBM • IP) Tandeau de Marsac (UC • IP) Dujon (GML • IP) d’Enfert (BPF • IP) Danchin Glaser Kunst Chetouani Coppée (GGB • IP) (GGB/GMP • IP) (BM/GMP • IP) (PT 2 • IP) Claudine Médigue Alain Viari David Sherman (GGB • IP/AGC) (ABI • P 6/ INRIA) (UB) BACELL Network Kenn Rudd Amos Bairoch (EU) (Miami U. ) (SIB) Stewart Cole Journées « Bioinformatique des Génopoles » - Lyon-Gerland, 22 octobre 2003
- Slides: 56