Formao de agrupamentos conceitos bsicos e algoritmos parte

Formação de agrupamentos: conceitos básicos e algoritmos (parte 2) prof. Luis Otavio Alvares INE/UFSC Parte desta apresentação é baseada em material do livro Introduction to Data Mining de Tan, Steinbach, Kumar e de material do prof. José Leomar Todesco (UFSC)
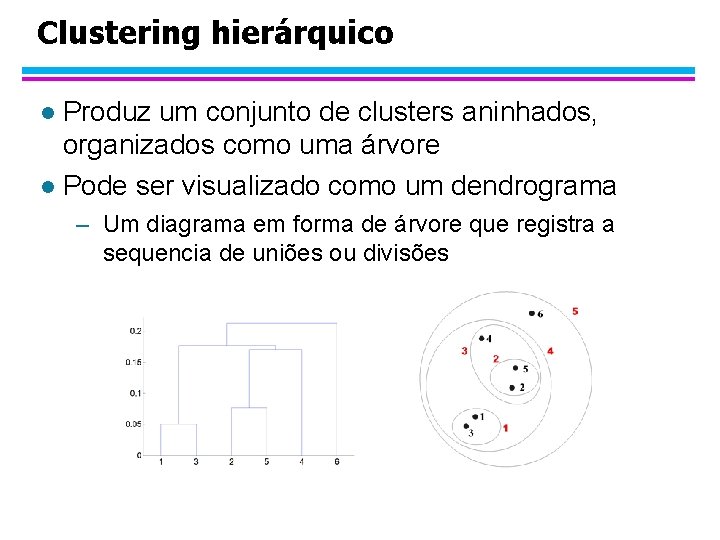
Clustering hierárquico Produz um conjunto de clusters aninhados, organizados como uma árvore l Pode ser visualizado como um dendrograma l – Um diagrama em forma de árvore que registra a sequencia de uniões ou divisões

Pontos fortes do clustering hierárquico l Não precisa assumir nenhum número particular de clusters – Qualquer número desejado de clusters pode ser obtido “cortando” o dendograma no nível adequado l Podem corresponder a taxonomias – Exemplo em biologia: o reino animal

Clustering hierárquico l Dois tipos principais – Aglomerativo: u Inicia com cada ponto como um cluster individual u A cada passo une o par de pontos mais próximos até que reste somente um cluster (ou k clusters) – Divisivo: u Inicia com um cluster contendo todos os pontos u A cada passo divide um cluster até que cada cluster contenha apenas um ponto (ou até que haja k clusters) l Os algoritmos tradicionais usam uma matriz de similaridade ou de proximidade (distância) – Unem ou dividem um cluster de cada vez
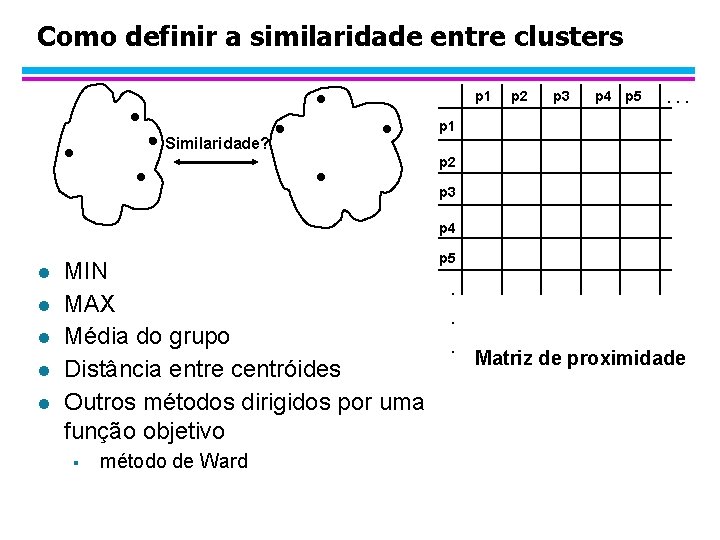
Como definir a similaridade entre clusters p 1 p 2 p 3 p 4 p 5 . . . p 1 Similaridade? p 2 p 3 p 4 l l l MIN MAX Média do grupo Distância entre centróides Outros métodos dirigidos por uma função objetivo § método de Ward p 5 . . . Matriz de proximidade
Como definir a similaridade entre clusters p 1 p 2 p 3 p 4 p 5 . . . p 1 p 2 p 3 p 4 l l l MIN MAX Média do grupo Distância entre centróides Outros métodos dirigidos por uma função objetivo § método de Ward p 5 . . . Matriz de proximidade
Como definir a similaridade entre clusters p 1 p 2 p 3 p 4 p 5 . . . p 1 p 2 p 3 p 4 l l l MIN MAX Média do grupo Distância entre centróides Outros métodos dirigidos por uma função objetivo § método de Ward p 5 . . . Matriz de proximidade
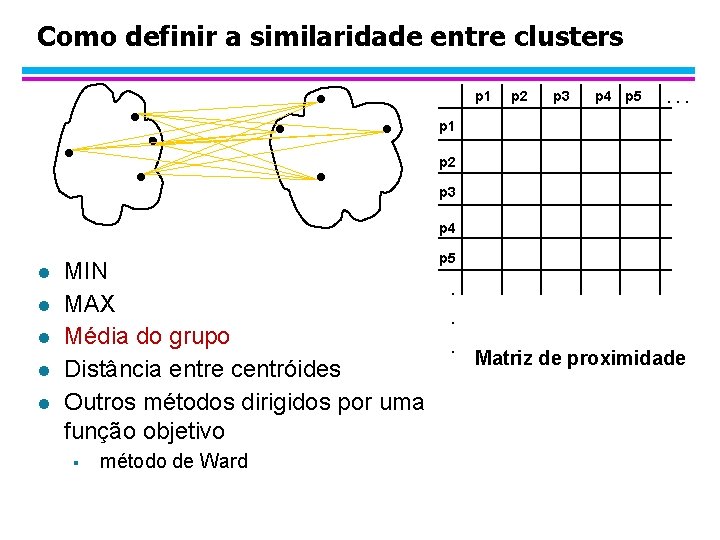
Como definir a similaridade entre clusters p 1 p 2 p 3 p 4 p 5 . . . p 1 p 2 p 3 p 4 l l l MIN MAX Média do grupo Distância entre centróides Outros métodos dirigidos por uma função objetivo § método de Ward p 5 . . . Matriz de proximidade
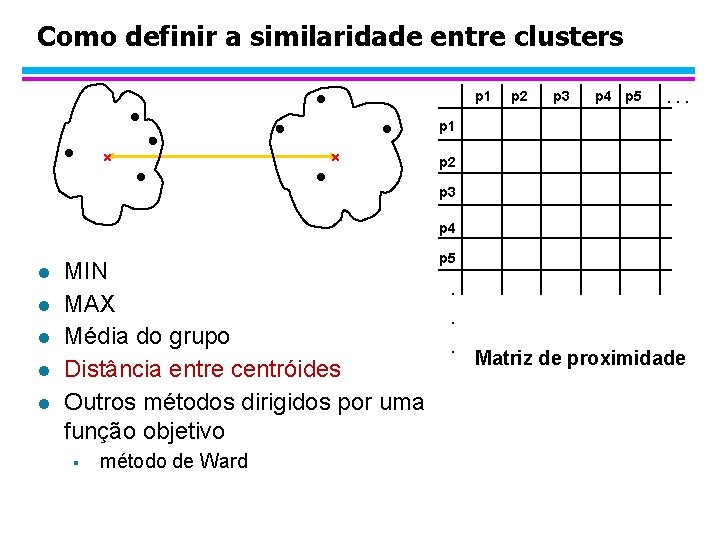
Como definir a similaridade entre clusters p 1 p 2 p 3 p 4 p 5 . . . p 1 p 2 p 3 p 4 l l l MIN MAX Média do grupo Distância entre centróides Outros métodos dirigidos por uma função objetivo § método de Ward p 5 . . . Matriz de proximidade

Algoritmo Geral de Agrupamento Hierárquico Aglomerativo Passo 1: Iniciar o agrupamento formado por grupos Unitários (cada ponto é um cluster) Passo 2: Encontre, no agrupamento corrente, o par de grupos de dissimilaridade (distância) mínima (= similaridade máxima) Passo 3: Construa um novo grupo pela fusão desse par de grupos de dissimilaridade mínima Passo 4: Atualize a matriz de dissimilaridades: suprima as linhas e as colunas correspondentes aos grupos fusionados e adicione uma linha e uma coluna correspondente as dissimilaridades entre o novo grupo e os grupos antigos Passo 5: Se todos os objetos estão grupados, pare; senão vá para o passo 2 Prof. Luis Otavio Alvares 10 10

Similaridade MIN ou Single Link l A similaridade entre dois clusters é baseada nos dois pontos mais similares (mais próximos) dos dois clusters diferentes – Determinada por um par de pontos, i. e. , por um link na matriz de proximidade. 1 2 3 4 5
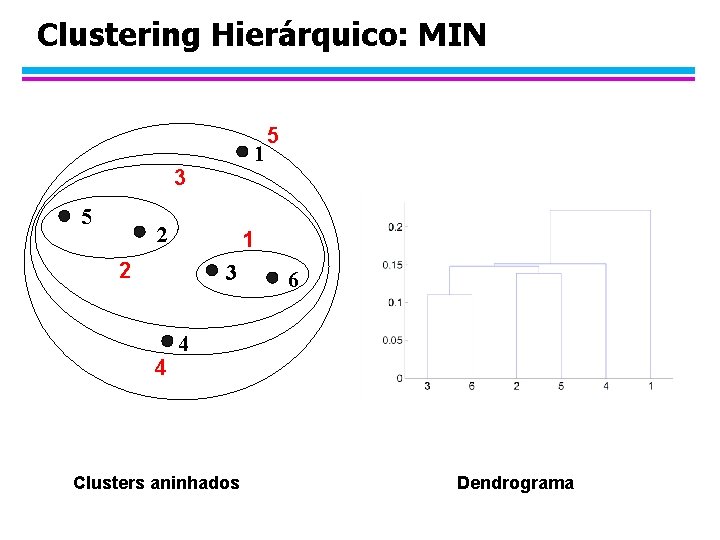
Clustering Hierárquico: MIN 1 3 5 2 1 2 3 4 5 6 4 Clusters aninhados Dendrograma
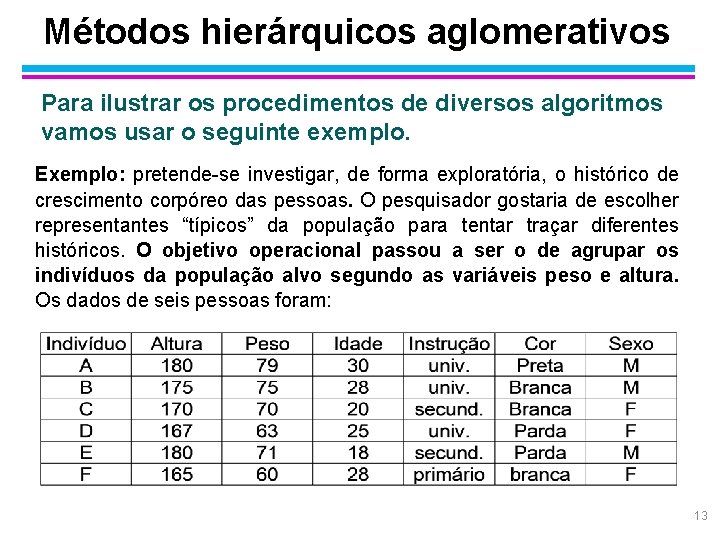
Métodos hierárquicos aglomerativos Para ilustrar os procedimentos de diversos algoritmos vamos usar o seguinte exemplo. Exemplo: pretende-se investigar, de forma exploratória, o histórico de crescimento corpóreo das pessoas. O pesquisador gostaria de escolher representantes “típicos” da população para tentar traçar diferentes históricos. O objetivo operacional passou a ser o de agrupar os indivíduos da população alvo segundo as variáveis peso e altura. Os dados de seis pessoas foram: 13
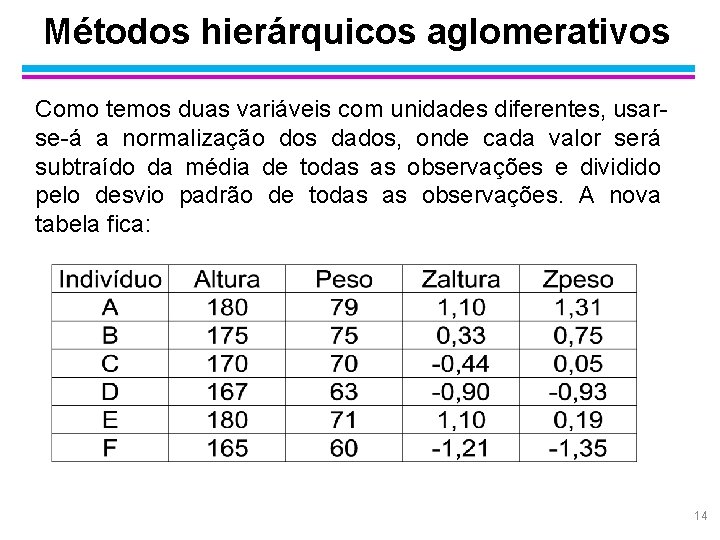
Métodos hierárquicos aglomerativos Como temos duas variáveis com unidades diferentes, usarse-á a normalização dos dados, onde cada valor será subtraído da média de todas as observações e dividido pelo desvio padrão de todas as observações. A nova tabela fica: 14
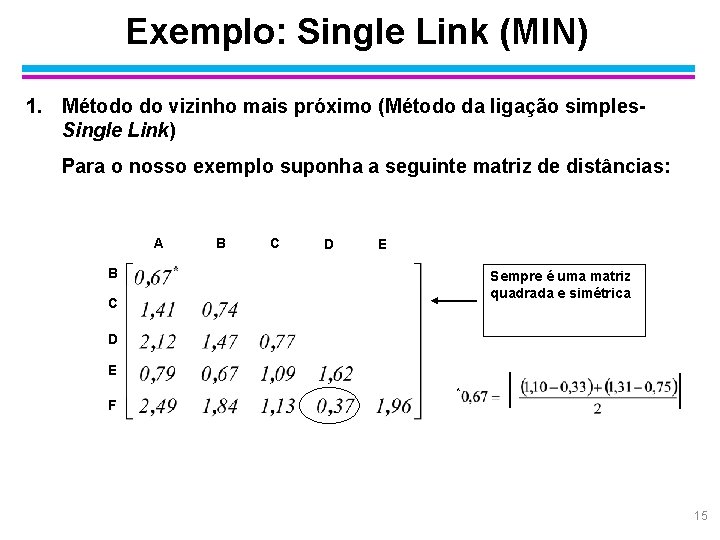
Exemplo: Single Link (MIN) 1. Método do vizinho mais próximo (Método da ligação simples. Single Link) Para o nosso exemplo suponha a seguinte matriz de distâncias: A B C D E B Sempre é uma matriz quadrada e simétrica C D E * F 15

Exemplo: Single Link § Passo 1: inicialmente, cada caso forma um grupo, isto é, temos 6 grupos iniciais. § Passo 2: olhando-se a matriz de distâncias, observa-se que as duas observações mais próximas são D e F, corresponde a uma distância de 0, 37, assim, esta duas observações são agrupadas, formando o primeiro grupo. Necessita-se, agora, das distâncias deste grupo aos demais. A partir da matriz de distâncias iniciais têm-se: Com isso, temos a seguinte matriz de distâncias: 16

Exemplo: Single Link A B C E DF § Passo 3: Agrupar A e B ao nível de 0, 67, e recalcular: A matriz resultante será: 17

Exemplo: Single Link C E DF AB § Passo 4: Agrupar AB com E ao nível de 0, 67, e recalcular: Matriz resultante: C DF DF ABE 18

Exemplo: Single Link § Passo 5: Agrupar C com ABE ao nível de 0, 74, e recalcular: Matriz resultante: DF ABCE § Passo 6: O último passo cria um único agrupamento contendo os 6 objetos, que serão similares a um nível de 0, 77. 19

Exemplo: Single Link Resumindo-se, temos: Distância Dendograma: 1, 0 0, 9 0, 8 0, 7 0, 6 0, 5 0, 4 0, 3 0, 2 0, 1 0, 0 D F A B E C 20

Pontos fortes da MIN Pontos originais • Pode tratar formas não-elípticas Dois Clusters

Limitações da MIN Pontos originais • Sensível a ruído e outliers Dois Clusters
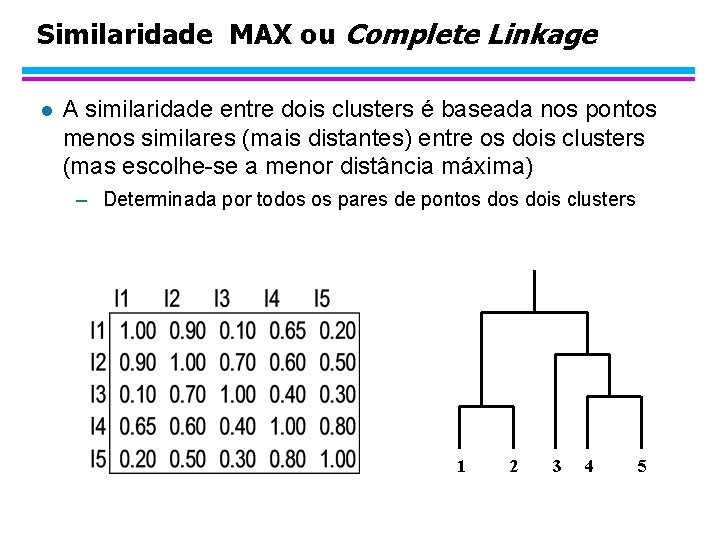
Similaridade MAX ou Complete Linkage l A similaridade entre dois clusters é baseada nos pontos menos similares (mais distantes) entre os dois clusters (mas escolhe-se a menor distância máxima) – Determinada por todos os pares de pontos dois clusters 1 2 3 4 5
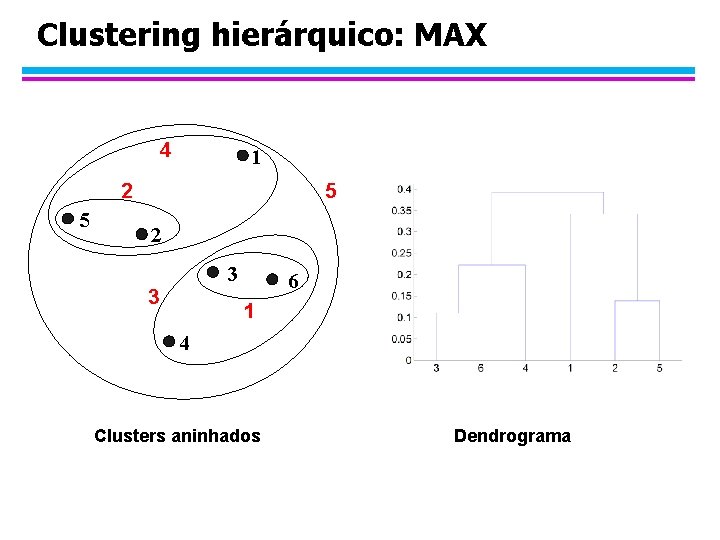
Clustering hierárquico: MAX 4 1 2 5 5 2 3 3 6 1 4 Clusters aninhados Dendrograma

Exemplo: Complete Linkage 2. Método do vizinho mais longe (Método da ligação completa – Complete Linkage) Define-se a distância entre os grupos X e Y como: Convém ressaltar que a fusão de dois grupos ainda é feita com os grupos mais parecidos (menor distância). § Passo 1: inicialmente, cada caso forma um grupo, isto é, temos 6 grupos iniciais. § Passo 2: olhando-se a matriz de distâncias, abaixo, observa-se que as duas observações mais próximas são D e F, corresponde a uma distância de 0, 37, assim, estas duas observações são agrupadas, formando o primeiro grupo. Necessita-se, agora, das distâncias deste grupo aos demais. A partir da matriz de distâncias iniciais tem-se: A B C D E F 25

Exemplo: Complete Linkage A B C E DF § Passo 3: Agrupar A e B ao nível de 0, 67, e recalcular: 26

Exemplo: Complete Linkage Temos: C E DF AB 27

Exemplo: Complete Linkage § Passo 4: Agrupar AB com E ao nível de 0, 79, e recalcular: Matriz resultante: C DF DF ABE 28

Exemplo: Complete Linkage § Passo 5: Agrupar C com DF ao nível de 1, 13, e recalcular: Matriz resultante: CDF ABE § Passo 6: O último passo cria um único agrupamento contendo os 6 objetos, que serão similares a um nível de 2, 49. 29

Exemplo: Complete Linkage Resumindo-se, temos: Dendograma: Distância 2, 5 1, 3 1, 2 1, 1 1, 0 0, 9 0, 8 0, 7 0, 6 0, 5 0, 4 0, 3 0, 2 0, 1 0, 0 D F C A B E

Ponto forte da MAX Pontos originais • Menos suscetível a ruído e outliers Dois Clusters

Limitações da MAX Pontos originais • Tendência a quebrar clusters grandes • Tendência a formar clusters esféricos Dois Clusters

Similaridade: Média do grupo l A proximidade de dois clusters é dada pela média da distância entre pares de pontos dois clusters. 1 2 3 4 5
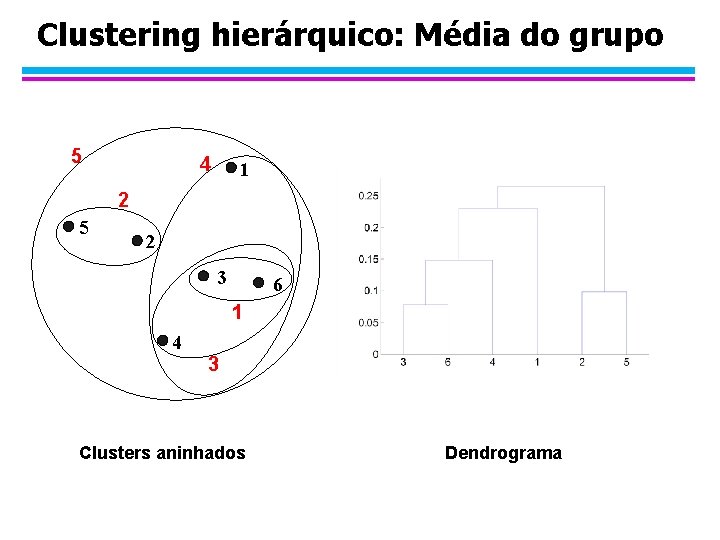
Clustering hierárquico: Média do grupo 5 4 1 2 5 2 3 6 1 4 3 Clusters aninhados Dendrograma

Exemplo: Clustering hierárquico: Média do grupo Dada a matriz de distâncias: A B C D E F § Passo 1: inicialmente, cada caso forma um grupo, isto é, temos 6 grupos iniciais. § Passo 2: olhando-se a matriz de distâncias, observa-se que as duas observações mais próximas são D e F, corresponde a uma distância de 0, 37, assim, esta duas observações são agrupadas, formando o primeiro grupo. Necessita-se, agora, das distâncias deste grupo aos demais. A partir da matriz de distâncias iniciais tem-se: 35

Exemplo: Average Linkage A B C E DF Com a obtenção da matriz de distâncias conclui-se o passo 2, que reuniu os pontos D e F, num nível igual à 0, 37. 36

Exemplo: Average Linkage Passo 3: Analisando a nova matriz de similaridade, nota-se que existem dois pares com a mesma proximidade: A com B e B com E. Recomenda-se selecionar aleatoriamente um dos pares e criar o novo grupo. Então, neste caso, agrupa-se A com B. § Temos: C E DF AB 37

Exemplo: Average Linkage § Passo 4: Agrupar AB com E ao nível de 0, 73, e recalcular: Matriz resultante: C DF DF ABE 38

Exemplo: Average Linkage § Passo 5: Agrupar C com DF ao nível de 0, 95, obtendo-se a partição (ABE, CDF) e recalcular: Matriz resultante: CDF ABE § Passo 6: O processo encerra reunindo num único grupo os conjuntos ABE e CDF, que são similares a um nível de 1, 64. 39
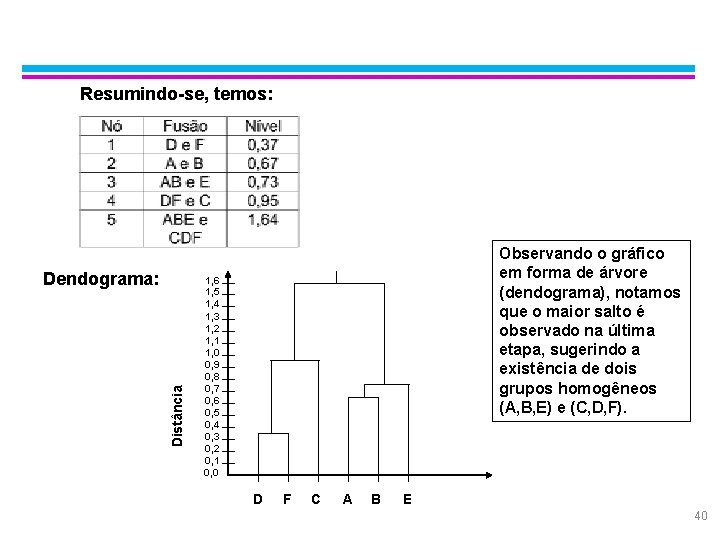
Exemplo: Average Linkage Resumindo-se, temos: Distância Dendograma: Observando o gráfico em forma de árvore (dendograma), notamos que o maior salto é observado na última etapa, sugerindo a existência de dois grupos homogêneos (A, B, E) e (C, D, F). 1, 6 1, 5 1, 4 1, 3 1, 2 1, 1 1, 0 0, 9 0, 8 0, 7 0, 6 0, 5 0, 4 0, 3 0, 2 0, 1 0, 0 D F C A B E 40

Clustering hierárquico: Média do grupo l Compromisso entre MAX e MIN l Ponto forte – Menos suscetível a ruído e outliers l Limitação – Tendência de gerar clusters esféricos

Método de Ward (Ward’s method) l A similaridade de dois clusters é baseada no aumento do erro quadrado quando dois clusters são unidos – Similar a média do grupo se a distância entre os pontos é a distância ao quadrado l Menos suscetível a ruído e outliers l Tendência de gerar clusters esféricos l Clustering Hierárquico análogo ao K-médias – Pode ser usado para inicializar o K-médias
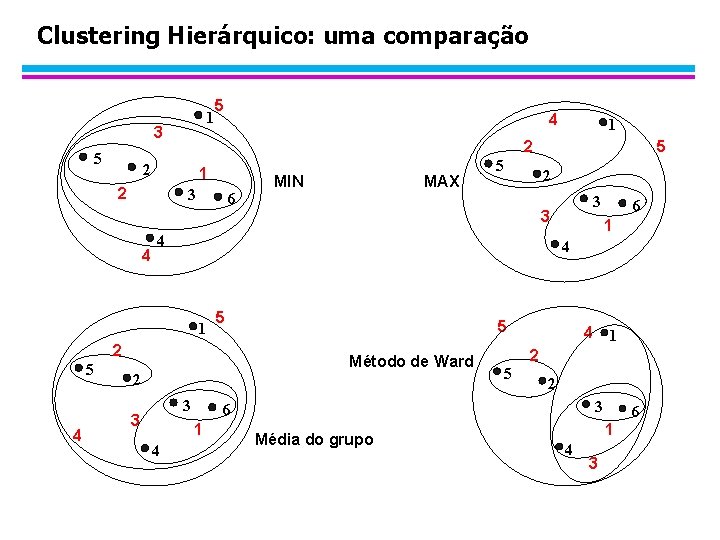
Clustering Hierárquico: uma comparação 1 3 5 5 1 2 3 6 MIN MAX 5 2 3 4 1 2 5 2 3 6 1 4 6 1 5 Método de Ward 3 3 4 2 4 5 4 1 5 1 2 2 4 4 Média do grupo 6 1 4 3

Clustering Hierárquico: necessidades de tempo e espaço l O(N 2) para espaço usando matriz de proximidade. – N é o número de pontos. l O(N 3) para o tempo em muitos casos – Tem N passos e em cada passo a matriz de tamanho N 2 tem que ser atualizada e percorrida – A complexidade pode ser reduzida para O(N 2 log(N) ) em algumas abordagens

DBSCAN Clustering baseado em densidade

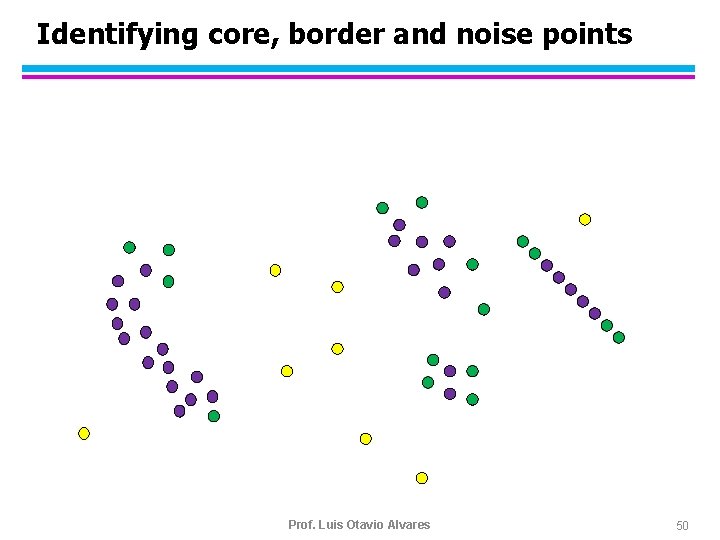
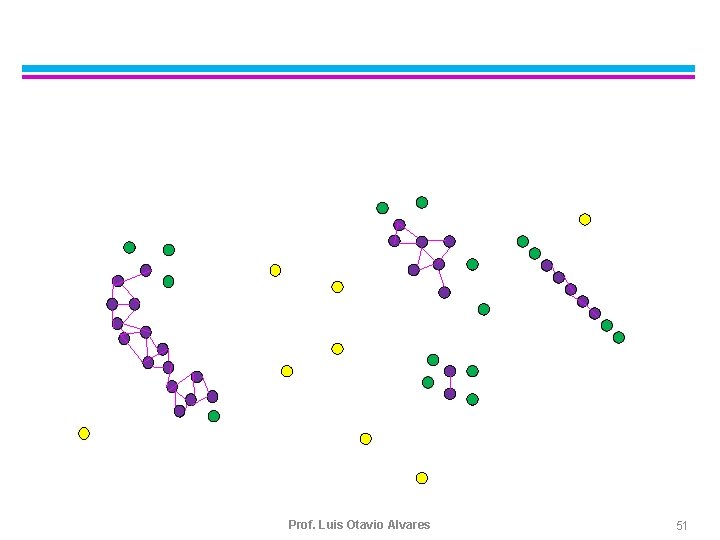
DBSCAN (1996) l DBSCAN é um algoritmo baseado em densidade – Densidade = número de pontos dentro de um raio especificado (Eps) – Um ponto é um core point se ele tem mais de um número especificado de pontos (Min. Pts) dentro do círculo de raio Eps u Estes são pontos que pertencem a um cluster – Um border point tem menos do que Min. Pts dentro do círculo de raio Eps, mas ele está na vizinhança (definida por Eps) de um core point – Um noise point é todo ponto que não é nem core point nem border point.
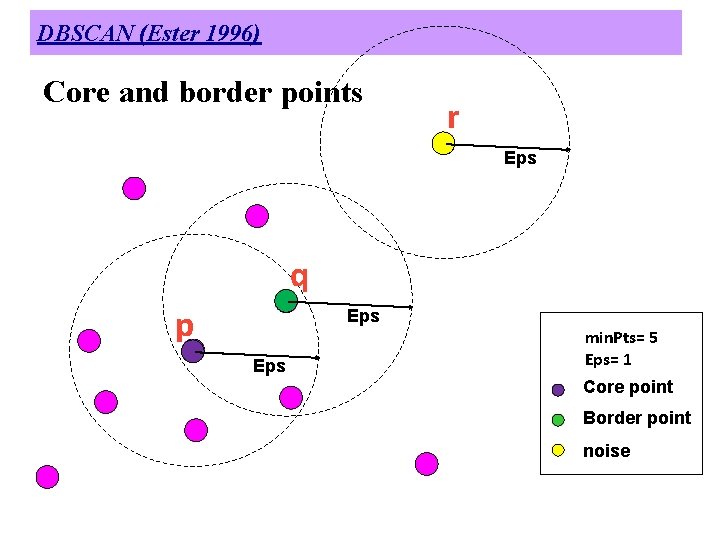
DBSCAN (Ester 1996) Core and border points r Eps q p Eps min. Pts= 5 Eps= 1 Core point Border point noise

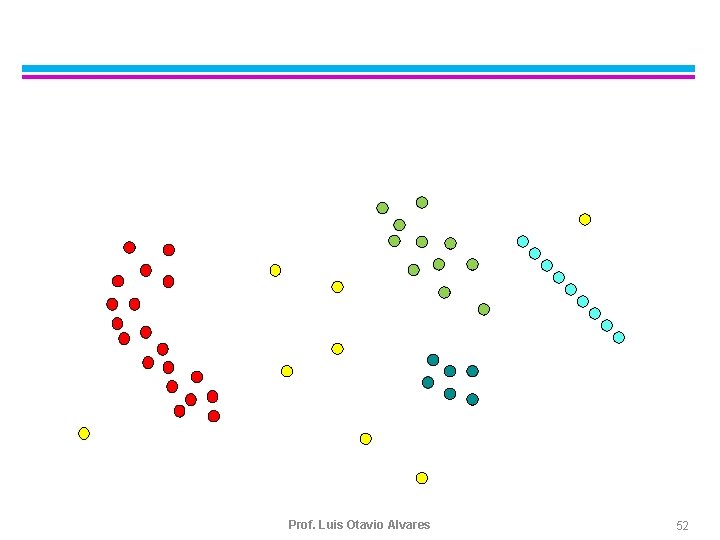
DBSCAN Algorithm Eliminate noise points l Perform clustering on the remaining points l

DBSCAN example Prof. Luis Otavio Alvares 49
Identifying core, border and noise points Prof. Luis Otavio Alvares 50
Prof. Luis Otavio Alvares 51
Prof. Luis Otavio Alvares 52
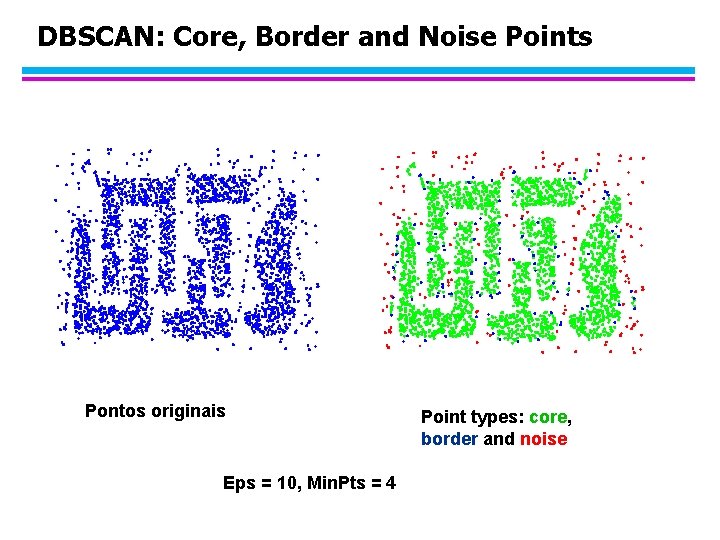
DBSCAN: Core, Border and Noise Points Pontos originais Eps = 10, Min. Pts = 4 Point types: core, border and noise

Quando o DBSCAN funciona bem Pontos originais Clusters • Tolerante a ruído • Pode tratar clusters de diferentes formas e tamanhos
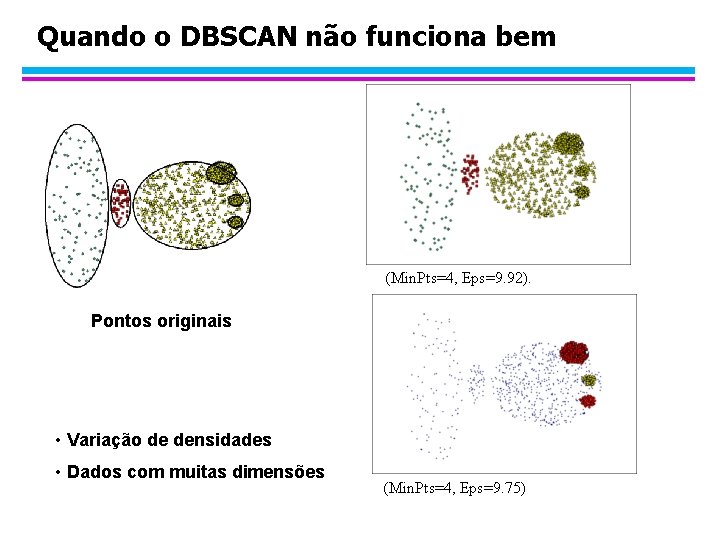
Quando o DBSCAN não funciona bem (Min. Pts=4, Eps=9. 92). Pontos originais • Variação de densidades • Dados com muitas dimensões (Min. Pts=4, Eps=9. 75)
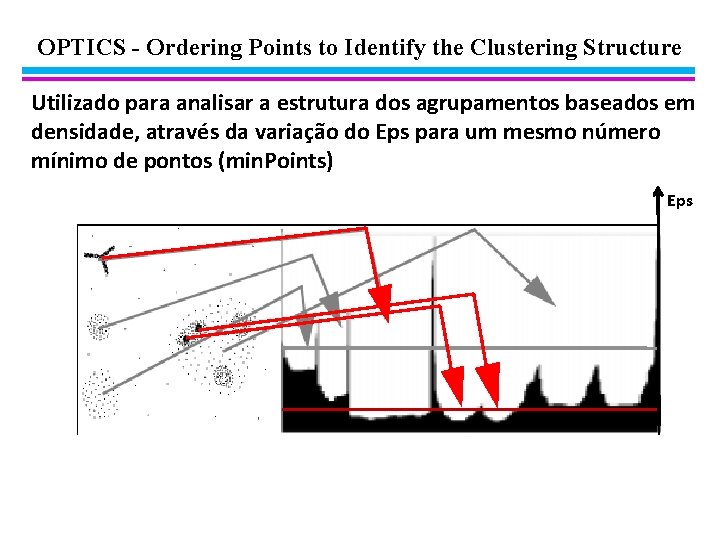
OPTICS - Ordering Points to Identify the Clustering Structure Utilizado para analisar a estrutura dos agrupamentos baseados em densidade, através da variação do Eps para um mesmo número mínimo de pontos (min. Points) Eps

Referências l Mac. Queen, J. B. (1967). "Some Methods for classification and Analysis of Multivariate Observations". Proceedings of 5 th Berkeley Symposium on Mathematical Statistics and Probability. University of California Press. pp. 281– 297 PAM l L. Kaufman and P. J. Rousueeuw. (1990) Finding Groups in Data: an Introduction to Cluster Analysis, John Wiley & Sons CLARANS l Raymond T. Ng, Jiawei Han(1994) Efficient and Effective Clustering Methods for Spatial Data Mining. Proceedings of the 20 th VLDB Conference, Santiago, Chile. pp 144 -155 DBSCAN l M. Ester, H-P. Kriegel, J. Sander, X. Xu. A Density-Based Algorithm for Discovering Clusters in Large Spatial Databases with Noise. Proc. KDD 1996. OPTICS l Mihael Ankerst, Markus M. Breunig, Hans-Peter Kriegel, Jörg Sander (1999). "OPTICS: Ordering Points To Identify the Clustering Structure". ACM SIGMOD international conference on Management of data. ACM Press. pp. 49– 60 K-means Hierárquicos l N. Jardine, R. Sibson. Mathematical Taxonomy. Wiley, New York, 1971.
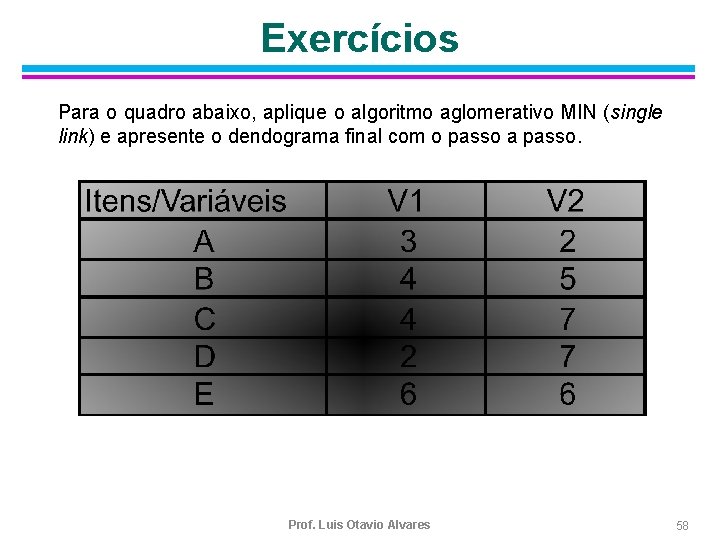
Exercícios Para o quadro abaixo, aplique o algoritmo aglomerativo MIN (single link) e apresente o dendograma final com o passo a passo. Prof. Luis Otavio Alvares 58
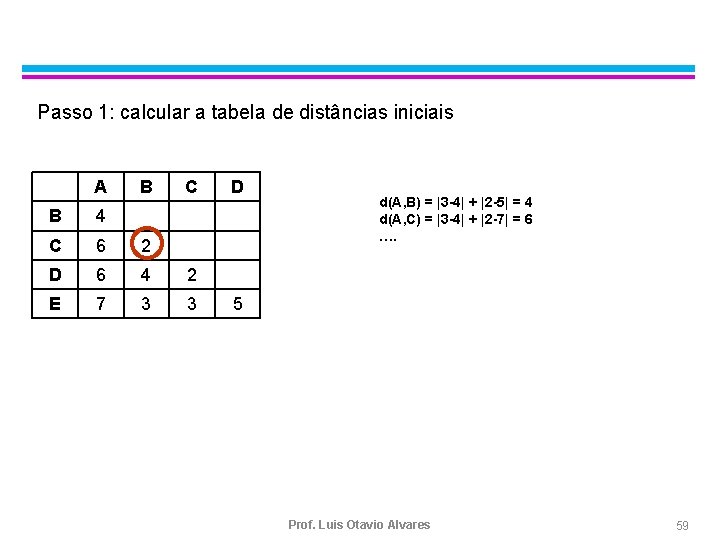
Passo 1: calcular a tabela de distâncias iniciais A B C B 4 C 6 2 D 6 4 2 E 7 3 3 D d(A, B) = |3 -4| + |2 -5| = 4 d(A, C) = |3 -4| + |2 -7| = 6 …. 5 Prof. Luis Otavio Alvares 59
- Slides: 59