ESERCIZI di BIOLOGIA MOLECOLARE A A 2004 2005

ESERCIZI di BIOLOGIA MOLECOLARE A. A 2004 -2005
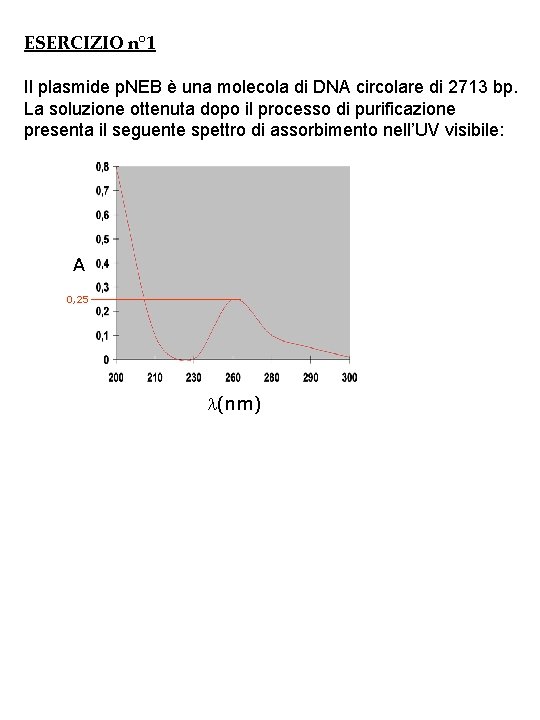
ESERCIZIO n° 1 Il plasmide p. NEB è una molecola di DNA circolare di 2713 bp. La soluzione ottenuta dopo il processo di purificazione presenta il seguente spettro di assorbimento nell’UV visibile: A 0, 25 l(nm)

1) Qual è la concentrazione MOLARE della soluzione? (d=cammino ottico=0, 3 cm) [C=30, 7 X 10 – 9 M=30, 7 n. M] 2) 1) Qual è la concentrazione in ngml? [C=55 ngml] Considerando che per la misura allo spettrofotometro, 5 ml della soluzione originaria sono stati diluiti in 95 ml di acqua, qual è la concentrazione molare della soluzione originaria? [C=614 X 10 – 9 M=614 n. M; C=1, 1 mgml] Quale sarebbe stata l’Assorbanza osservata se la misura fosse stata eseguita sulla soluzione originaria? [ A = 4, 99] Considerando che il volume della soluzione originaria rimasta è 30 ml, quanti mg totali di DNA abbiamo? [DNATOT= 33 mg] 1) 2)

ESERCIZIO n° 2 Avendo 815 · 10 -6 g. di u oligonucleotide a singolo filamento (primer) lungo 24 nt, in quanti ml di acqua è necessario scioglierli per ottenere una soluzione 100 m. M? [V=1029 ml=1, 3 ml] Diluiamo 1 ml della soluzione in 99 ml di acqua. Quale risulterà l’assorbanza a l=260 nm di tale soluzione? [ A=0, 24] ESERCIZIO n° 3 Il Servizio di Sequenziamento richiede per eseguire la reazione -500 ng. di campione da sequenziare -6, 4 pmol dell’oligonucleotide utilizzato come primer. 1)Quanti ml di una soluzione 125 n. M di un plasmidio lungo 3215 bp da sequenziare devo inviare? [ 1, 88 ml ] 2)Quanti ml di oligonucleotide 10 m. M? [ 0, 64 ml ]

ESERCIZIO n° 4 Quanto misura la lunghezza in nm di una molecola di DNA lineare in forma B costituita da 9824 bp? [ L=3340, 16 nm=3, 34 mm ] Quanti giri di elica contiene? [n°giri=982] Se la stessa molecola viene posta in alcool, quindi in condizioni di scarsa umidità, quale modificazione strutturale interviene? [forma A] Di quanto varieranno lunghezza in nm e numero di giri dell’elica? [L=2515 nm=2, 515 mm ; n° giri=893] ESERCIZIO n° 5 Qual è il peso molecolare (PM) di una molecola di DNA ds (double strand)di 3421 bp? [PM= 2257869 Da] Quale invece il peso molecolare di un singolo filamento di DNA di 1750 nucleotidi? [PM=577500 Da] ESERCIZIO n° 6 Se una soluzione contenente tre frammenti di DNA lunghi rispettivamente 1600 bp, 650 bp e 1105 bp, viene sottoposta ad elettroforesi su gel di agarosio, quale sarà, a partire dal polo positivo, l’ordine delle bande osservate al termine della corsa?
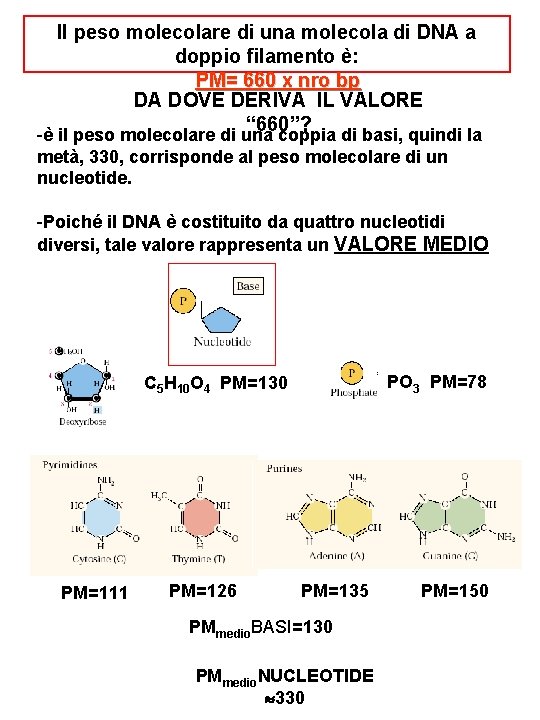
Il peso molecolare di una molecola di DNA a doppio filamento è: PM= 660 x nro bp DA DOVE DERIVA IL VALORE “ 660”? -è il peso molecolare di una coppia di basi, quindi la metà, 330, corrisponde al peso molecolare di un nucleotide. -Poiché il DNA è costituito da quattro nucleotidi diversi, tale valore rappresenta un VALORE MEDIO PO 3 PM=78 C 5 H 10 O 4 PM=130 PM=111 PM=126 PM=135 PMmedio. BASI=130 PMmedio. NUCLEOTIDE 330 PM=150

ESERCIZIO n° 7 Un plasmide di 3000 bp viene sottoposto ad una serie di restrizioni analitiche danno i seguenti risultati visualizzati con gel-elettroforesi: RI o Ec 1) m Ba HI RI I o Ec m. H Ba Kb Quanti siti di restrizione ha Eco. RI? [2] 2) Quanti siti di restrizione ha Bam. HI? [2] 3) Quali sono le distanze reciproche tra i siti? Disegnare la mappa di restrizione.
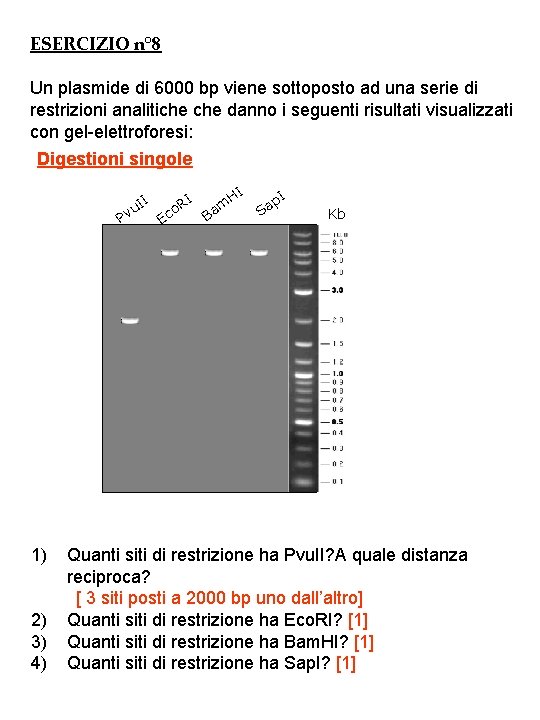
ESERCIZIO n° 8 Un plasmide di 6000 bp viene sottoposto ad una serie di restrizioni analitiche danno i seguenti risultati visualizzati con gel-elettroforesi: Digestioni singole II vu P 1) 2) 3) 4) Ec I o. R HI B am I p Sa Kb Quanti siti di restrizione ha Pvu. II? A quale distanza reciproca? [ 3 siti posti a 2000 bp uno dall’altro] Quanti siti di restrizione ha Eco. RI? [1] Quanti siti di restrizione ha Bam. HI? [1] Quanti siti di restrizione ha Sap. I? [1]
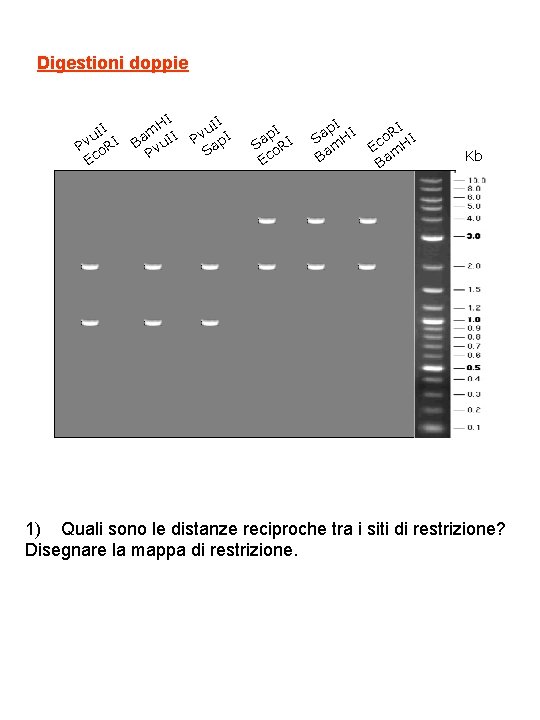
Digestioni doppie I u. I I v P o. R Ec HI m I Ba vu. I P II u Pv ap. I S p. I I a S o. R Ec p. I I a H S m Ba I o. R HI c E m Ba Kb 1) Quali sono le distanze reciproche tra i siti di restrizione? Disegnare la mappa di restrizione.

ESERCIZIO n° 9 Un frammento di DNA lineare lungo 5000 bp viene sottoposto ad una serie di restrizioni analitiche danno i seguenti risultati visualizzati con gel-elettroforesi: RI o Ec Ba m HI RI I o Ec m. H Ba Kb 1) Quanti siti di restrizione ha Eco. RI? [1] 2) Quanti siti di restrizione ha Bam. HI? [1] 3) Quali sono le distanze reciproche tra i siti? Disegnare la mappa di restrizione del frammento.

ESERCIZIO n° 10 Il plasmide A, lungo 4000 bp viene tagliato con Bam. HI e il risultato della restrizione viene visualizzato tramite gelelettroforesi: I m. H Ba Kb 1) 2) Quanti siti di restrizione ha Bam. HI? [2] Qual è la loro posizione reciproca? [1000 bp di distanza] Supponiamo di recuperare e purificare il frammento di restrizione più lungo. Avendo digerito 4 mg di plasmide A, se al termine della purificazione del frammento di 3000 bp, la soluzione ottenuta presenta una A 260 nm=0, 4, quanti ng di DNA sono stati persi nei vari passaggi rispetto alla resa teorica? [ DNA perduto=1260 ng]

Il frammento di 3000 bp viene utilizzato come vettore di clonaggio per l’inserzione di un frammento di DNA di 178 bp ottenuto a sua volta da un secondo plasmide per restrizione Bam. HI-Nde. I. 1) Quale sarà la lunghezza in bp del nuovo costrutto? [3178 bp] 2) Quale sarà il risultato di una successiva digestione del nuovo costrutto con Bam. HI? [il costrutto circolare viene linearizzato] 3)Nella reazione di ligazione, vettore e inserto devono essere miscelati in rapporto molare 1: 3; utilizzando 100 ng di vettore, quanti ng di inserto sono necessari? [quantità inserto=17, 62 ng] Se la soluzione dell’inserto di 178 bp a disposizione presenta lo spettro di assorbimento nell’UV visibile rappresentato in figura, quanti ml ne devono essere utilizzati? [V= 0, 5 ml] A 0, 15 l(nm)

ESERCIZIO n° 11 Dobbiamo preparare 50 ml di un buffer di trascrizione(10 X) così costituito: 500 m. M KCl 200 ml Tris-HCl 50 m. M Mg. Cl 2 Avendo a disposizione i seguenti stock concentrati Tris-Hcl 1 M KCl 2 M Mg. Cl 2 1 M Quanti ml di ciascuno stock devono essere utilizzati? [KCl 12, 5 ml; Tris-HCl 10 ml; Mg. Cl 2 2, 5 ml; si aggiungono 25 ml di acqua] Considerando che il volume di ciascuno stock è 25 ml e che le tre sostanze hanno i seguenti PM KCL PM=74, 56 uma Mg. Cl 2 PM=203. 32 uma Tris-HCl PM=157. 64 uma quanti g. di ciascuna sostanza sono stati pesati per preparare i tre stock? [KCl g. 3, 728; Mg. Cl 2 g. 5, 083; Tris-HCl g. 3, 941] Quanti g. di ciascuna sostanza sarebbero serviti per preparare il buffer direttamente dalle polveri? [KCl g. 1, 864; Mg. Cl 2 g. 0, 5; Tris-HCl g. 1, 576]

ESERCIZIO n° 12 Per ottenere un frammento di DNA di 850 bp, esso viene amplificatotramite PCR e gel purificato. Si allestiscono 4 reazioni di PCR, ciascuna avente un Volume di 50 ml. Considerando che a PCR ultimata la concentrazione di DNA n soluzione è in ciascun tubo 10 ngml e che l’efficienza della procedura di gel purificazione è del 70 %, quale sarà la concentrazione molare dei 50 ml di soluzione finale ottenuti? Quanti mg. totali di DNA si ottengono? [c=50 x 10 -9 M =50 n. M; mg. DNA 1, 4]
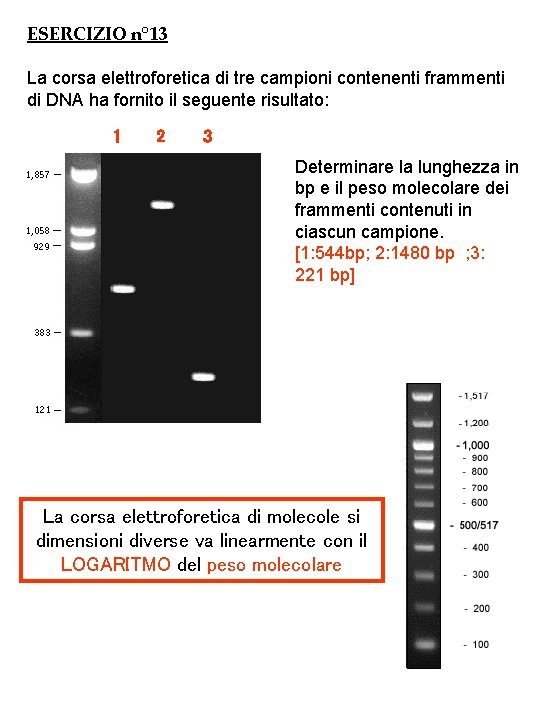
ESERCIZIO n° 13 La corsa elettroforetica di tre campioni contenenti frammenti di DNA ha fornito il seguente risultato: 1 2 3 Determinare la lunghezza in bp e il peso molecolare dei frammenti contenuti in ciascun campione. [1: 544 bp; 2: 1480 bp ; 3: 221 bp] La corsa elettroforetica di molecole si dimensioni diverse va linearmente con il LOGARITMO del peso molecolare
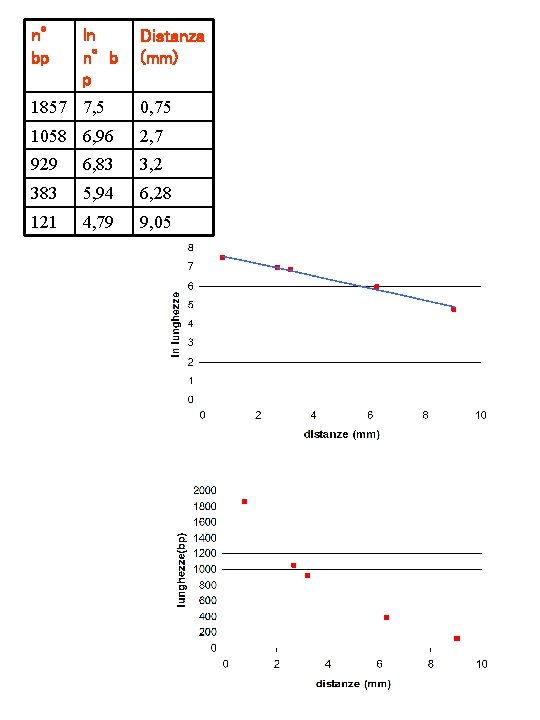
n° bp ln n°b p Distanza (mm) 1857 7, 5 0, 75 1058 6, 96 2, 7 929 6, 83 3, 2 383 5, 94 6, 28 121 4, 79 9, 05
- Slides: 16