Esempio del fingerprint del DNA con una sonda









- Slides: 23

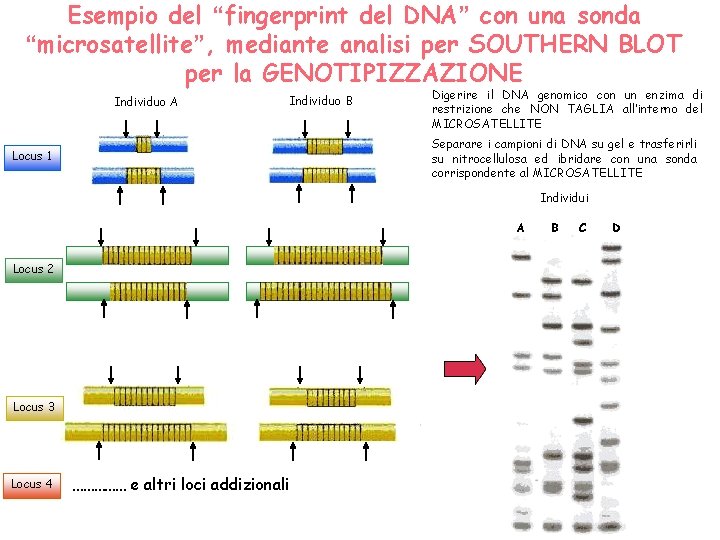
Esempio del “fingerprint del DNA” con una sonda “microsatellite”, mediante analisi per SOUTHERN BLOT per la GENOTIPIZZAZIONE Individuo A Individuo B Digerire il DNA genomico con un enzima di restrizione che NON TAGLIA all’interno del MICROSATELLITE Separare i campioni di DNA su gel e trasferirli su nitrocellulosa ed ibridare con una sonda corrispondente al MICROSATELLITE Locus 1 Individui A Locus 2 Locus 3 Locus 4 …………… e altri loci addizionali B C D

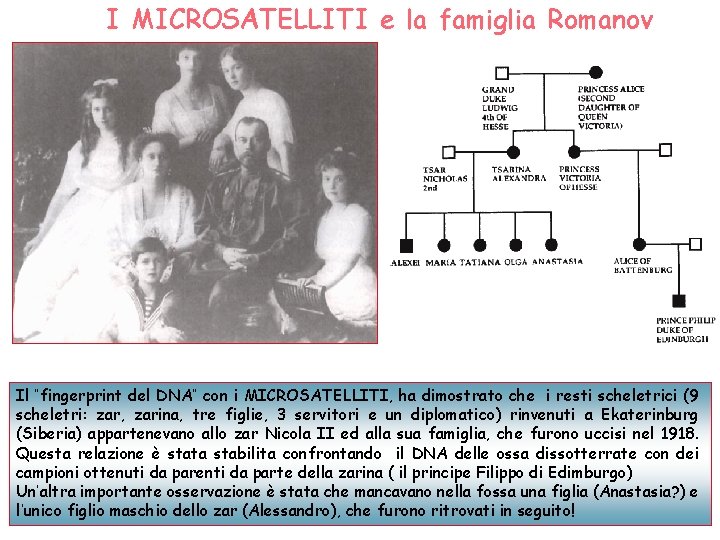
I MICROSATELLITI e la famiglia Romanov Il “fingerprint del DNA” con i MICROSATELLITI, ha dimostrato che i resti scheletrici (9 scheletri: zar, zarina, tre figlie, 3 servitori e un diplomatico) rinvenuti a Ekaterinburg (Siberia) appartenevano allo zar Nicola II ed alla sua famiglia, che furono uccisi nel 1918. Questa relazione è stata stabilita confrontando il DNA delle ossa dissotterrate con dei campioni ottenuti da parenti da parte della zarina ( il principe Filippo di Edimburgo) Un’altra importante osservazione è stata che mancavano nella fossa una figlia (Anastasia? ) e l’unico figlio maschio dello zar (Alessandro), che furono ritrovati in seguito!

I MINISATELLITI ed il “ fingerprint del DNA” • Anche i MINISATELLITI, come i microsatelliti, sono loci distinguibili per le dimensioni piuttosto che per sequenza; possono variare da 1 a 20 kb (20 -100 bp ripetuti da 50 a 200 volte) • Nel 1985 Alec Jeffreys dimostò che ogni locus minisatellite è altamente polimorfico ed i minisatelliti si trovano distribuiti in tutto il genoma. • Molti loci minisatellite possono essere individuati con la stessa tecnica di PCR descritta per i microsatelliti, ma possono anche essere individuati per Southern; le sonde che riconoscono i minisatelliti sono efficaci per ottenere "il fingerprint del DNA". • per identificare i polimorfismi di lunghezza ai loci usando enzimi di restrizione e Southern blot si usano enzimi che non tagliano dentro il minisatellite ma ai lati. I frammenti sono poi separati su gel di agarosio, trasferiti ed ibridati con la sonda minisatellite. • I minisatelliti forniscono un'immagine generale dell'intero genoma piuttosto che di un singolo locus • La probabilità che due individui non imparentati abbiano un GENOTIPO IDENTICO a 10 loci contenenti lo stesso minisatellite ha una bassissima probabilità ( è sufficiente usare 2 MINISATELLITI non correlati e analizzare circa 24 loci genomici (24 bande di ibridazione) per definire con certezza se 2 campioni di DNA appartengano alla stessa persona oppure no. Sono loci polimorfici e sono l'ideale per la correlazione genetica tra due individui oppure tra un individuo e una traccia biologica di DNA trovata sulla scena di un crimine.

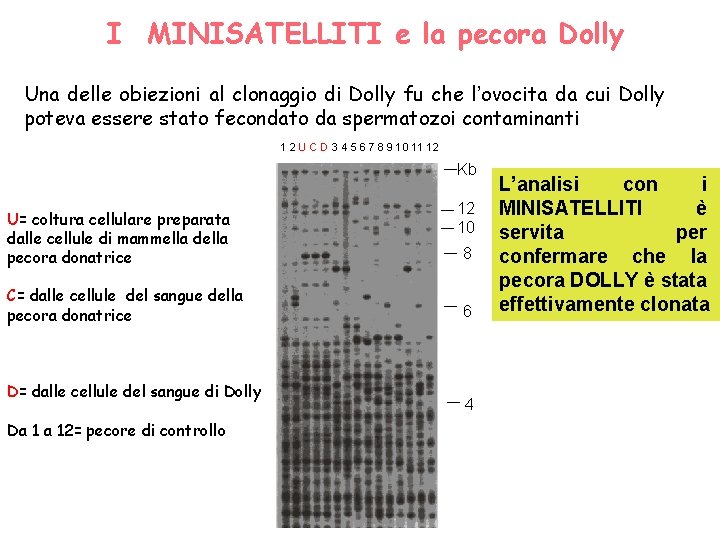
I MINISATELLITI e la pecora Dolly Una delle obiezioni al clonaggio di Dolly fu che l’ovocita da cui Dolly poteva essere stato fecondato da spermatozoi contaminanti 1 2 U C D 3 4 5 6 7 8 9 10 11 12 Kb U= coltura cellulare preparata dalle cellule di mammella della pecora donatrice C= dalle cellule del sangue della pecora donatrice D= dalle cellule del sangue di Dolly Da 1 a 12= pecore di controllo 12 10 8 6 4 L’analisi con i MINISATELLITI è servita per confermare che la pecora DOLLY è stata effettivamente clonata

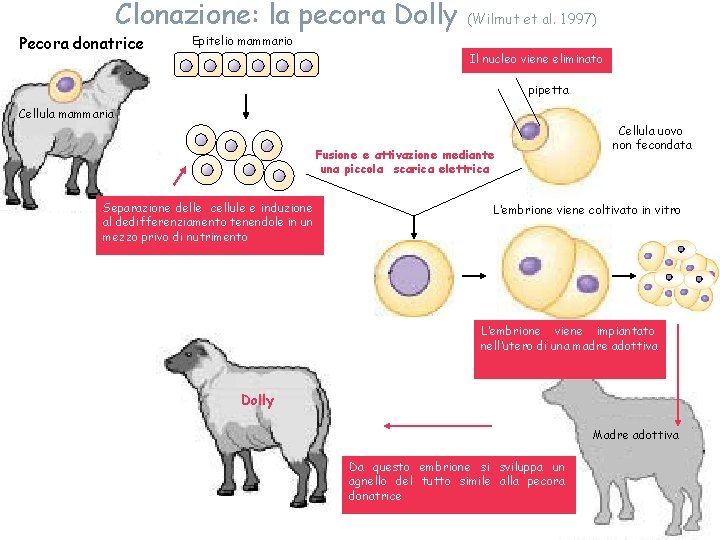
Clonazione: la pecora Dolly Pecora donatrice (Wilmut et al. 1997) Epitelio mammario Il nucleo viene eliminato pipetta Cellula mammaria Fusione e attivazione mediante una piccola scarica elettrica Separazione delle cellule e induzione al dedifferenziamento tenendole in un mezzo privo di nutrimento Cellula uovo non fecondata L’embrione viene coltivato in vitro L’embrione viene impiantato nell’utero di una madre adottiva Dolly Madre adottiva Da questo embrione si sviluppa un agnello del tutto simile alla pecora donatrice

Il primo caso risolto con la genetica forense 1985: MINISATELLITI, inizia l’era del DNA typing Il primo caso criminale risolto mediante DNA typing: il signor Colin Pitchfork 1983: Lynda Mann, 15 anni, viene violentata e uccisa nel Leichestershire (UK) 1986: Dawn Ashworth, 15 anni, viene violentata e uccisa nella stessa zona Il modus operandi nei due delitti era lo stesso ed il gruppo sanguigno (gruppo A), determinato dalle tracce di liquido seminale, era il medesimo. 1986: Richard Buckland, un ragazzo del posto, venne incriminato dei due delitti, ma l’analisi del DNA mediante fingerprinting con i minisatelli (da poco scoperti) rivelò che egli era innocente. Circa 5000 individui nel Leichestershire possedevano il gruppo sanguigno A. Si organizzò uno screening di massa ed in nessun caso il DNA fingerprinting dei 5000 individui corrispondeva a quello dell’assassino. 1987: Per un puro caso, si venne a sapere che una persona del posto, un certo Colin Pitchfork, aveva chiesto ad un amico ed ottenuto di partecipare allo screening in sua vece. Il signor Pitchfork venne invitato a donare il sangue ed il profilo del suo DNA risultò identico a quello del DNA raccolto sulla scena dei due delitti.

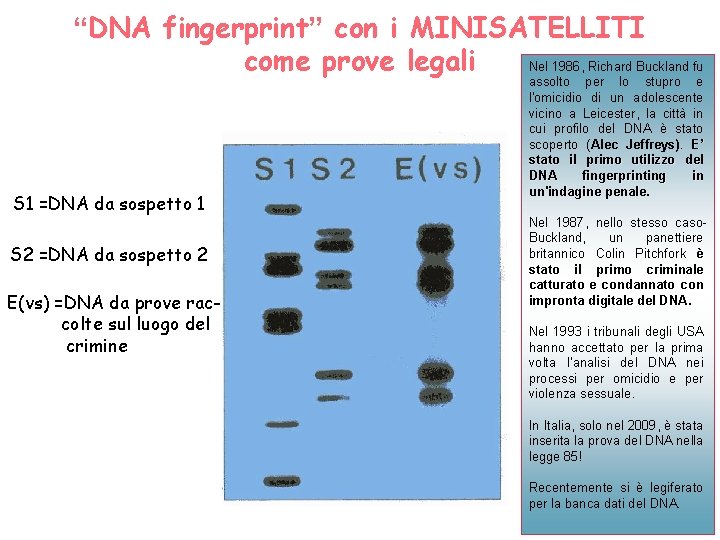
“DNA fingerprint” con i MINISATELLITI come prove legali Nel 1986, Richard Buckland fu S 1 =DNA da sospetto 1 S 2 =DNA da sospetto 2 E(vs) =DNA da prove raccolte sul luogo del crimine assolto per lo stupro e l'omicidio di un adolescente vicino a Leicester, la città in cui profilo del DNA è stato scoperto (Alec Jeffreys). E’ stato il primo utilizzo del DNA fingerprinting in un'indagine penale. Nel 1987, nello stesso caso. Buckland, un panettiere britannico Colin Pitchfork è stato il primo criminale catturato e condannato con impronta digitale del DNA. Nel 1993 i tribunali degli USA hanno accettato per la prima volta l’analisi del DNA nei processi per omicidio e per violenza sessuale. In Italia, solo nel 2009, è stata inserita la prova del DNA nella legge 85! Recentemente si è legiferato per la banca dati del DNA.

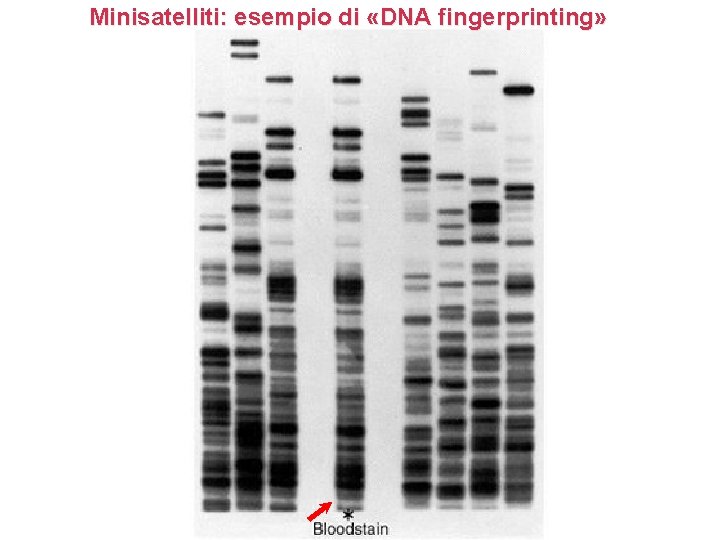
Minisatelliti: esempio di «DNA fingerprinting»

VANTAGGI degli STR (microsatelliti) rispetto ai VNTR (minisatelliti) Tecnicamente gli STR, in confronto con altri marcatori, presentano il vantaggio di essere: 1. Numerosi 2. Equamente distribuiti in tutta la parte eucromatica del genoma 3. Questa relativa facilità di studio ha portato ad un rapido incremento del numero degli STRs esaminati Catalogazione standard: - ad esempio D 12 S 324, dove 12 è il cromosoma sul quale il marker è localizzato e 324 è un codice identificativo Altamente polimorfici e quindi informativi 4. Analizzabili facilmente tramite PCR Bennett - Demystified. . . Microsatellites. J Clin Pathol: Mol Pathol 2000, 53: 177 -183


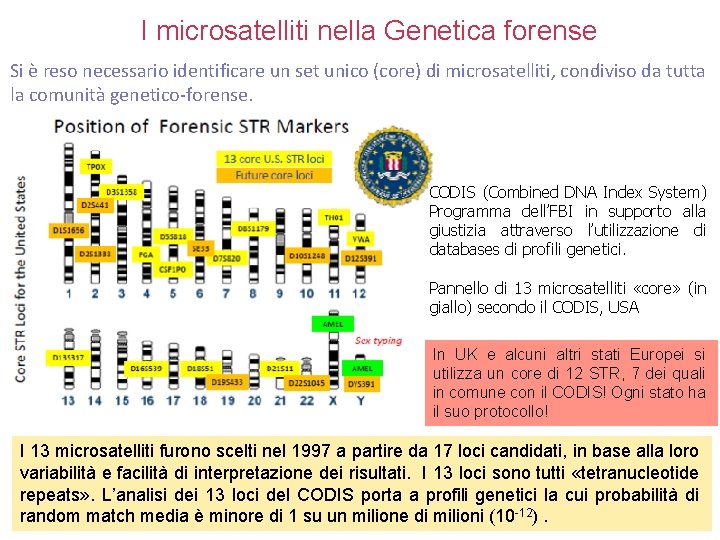
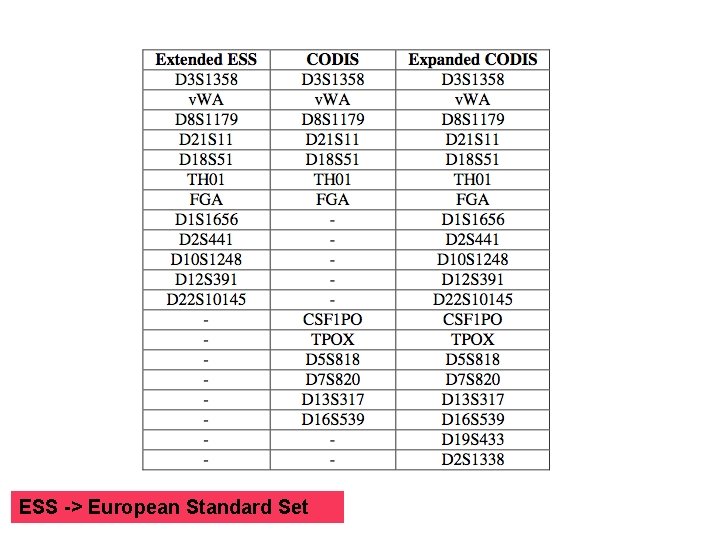
I microsatelliti nella Genetica forense Si è reso necessario identificare un set unico (core) di microsatelliti, condiviso da tutta la comunità genetico-forense. CODIS (Combined DNA Index System) Programma dell’FBI in supporto alla giustizia attraverso l’utilizzazione di databases di profili genetici. Pannello di 13 microsatelliti «core» (in giallo) secondo il CODIS, USA In UK e alcuni altri stati Europei si utilizza un core di 12 STR, 7 dei quali in comune con il CODIS! Ogni stato ha il suo protocollo! I 13 microsatelliti furono scelti nel 1997 a partire da 17 loci candidati, in base alla loro variabilità e facilità di interpretazione dei risultati. I 13 loci sono tutti «tetranucleotide repeats» . L’analisi dei 13 loci del CODIS porta a profili genetici la cui probabilità di random match media è minore di 1 su un milione di milioni (10 -12).

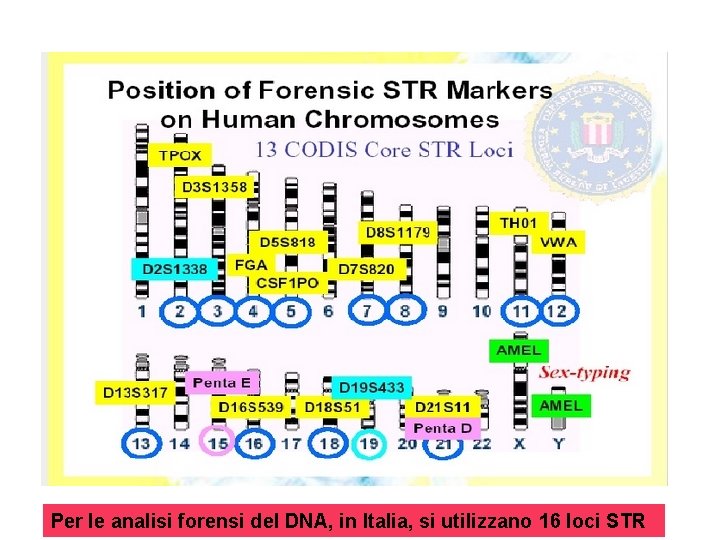
Per le analisi forensi del DNA, in Italia, si utilizzano 16 loci STR

ESS -> European Standard Set

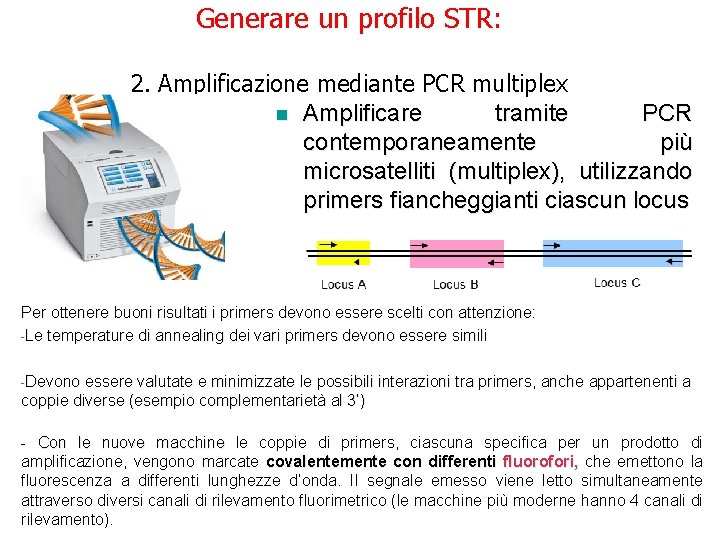
Generare un profilo STR: 2. Amplificazione mediante PCR multiplex n Amplificare tramite PCR contemporaneamente più microsatelliti (multiplex), utilizzando primers fiancheggianti ciascun locus Per ottenere buoni risultati i primers devono essere scelti con attenzione: -Le temperature di annealing dei vari primers devono essere simili -Devono essere valutate e minimizzate le possibili interazioni tra primers, anche appartenenti a coppie diverse (esempio complementarietà al 3’) - Con le nuove macchine le coppie di primers, ciascuna specifica per un prodotto di amplificazione, vengono marcate covalentemente con differenti fluorofori, che emettono la fluorescenza a differenti lunghezze d’onda. Il segnale emesso viene letto simultaneamente attraverso diversi canali di rilevamento fluorimetrico (le macchine più moderne hanno 4 canali di rilevamento).

Microarrays di DNA, c. DNA e oligonucleotidi

Tecnologia degli “array” di DNA Un array di DNA è una grande collezione di frammenti di DNA disposti in file ordinate su un supporto solido chiamato “chip”. I chip sono formati da moltissime molecole di DNA (detti sonde) depositate in una posizione nota su un supporto a formare una griglia (da cui il nome array) che consente di identificarle in MODO UNIVOCO. Il supporto, di solito, è un vetrino da microscopio che ha le dimensioni, più o meno, di un francobollo. Ogni sonda è costituita DNA a singola elica che può corrispondere al c. DNA di un gene, ad una sequenza genomica oppure ad un oligonucleotide (c. DNA o genomico). Per costruire un array si possono: • usare cloni di c. DNA prelevati direttamente da micropozzetti • produrre frammenti di DNA per PCR che saranno poi depositate in posizioni specifiche su un supporto solido usandone microscopiche gocce • sintetizzare oligonucleotidi direttamente su un supporto solido che corrispondono a porzioni di geni specifici 3 tipi diversi di array macroarray microarray di oligonucleotidi

Macroarray Dopo la creazione di una genoteca di c. DNA, una macchina equipaggiata con molteplici punte raccoglie il c. DNA da micropozzetti e lo deposita su una membrana di nylon o su altri tipi di supporto formando un “array”. Per costruire un macroarray si possono così depositare fino a 20000 cloni da una genoteca La miscela di ! a t a r e p c. DNA che deve essere analizzata u S è marcata RADIOATTIVAMENTE e quindi il segnale d’ibridazione è visibile per autoradiografia.

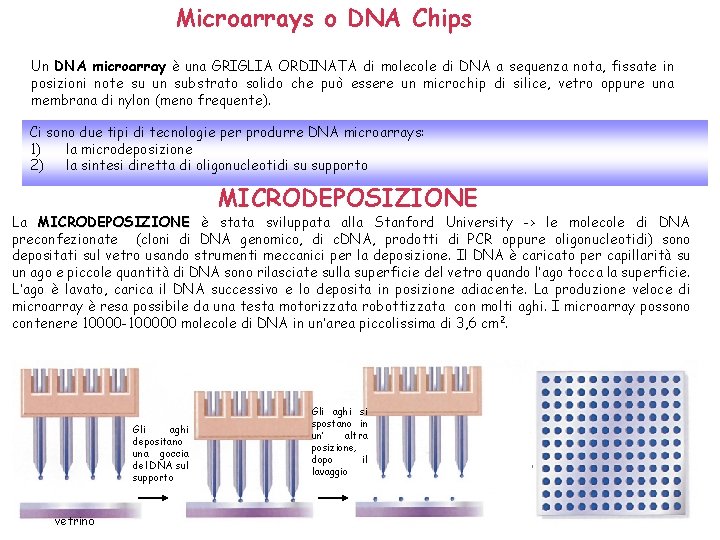
Microarrays o DNA Chips Un DNA microarray è una GRIGLIA ORDINATA di molecole di DNA a sequenza nota, fissate in posizioni note su un substrato solido che può essere un microchip di silice, vetro oppure una membrana di nylon (meno frequente). Ci sono due tipi di tecnologie per produrre DNA microarrays: 1) la microdeposizione 2) la sintesi diretta di oligonucleotidi su supporto MICRODEPOSIZIONE La MICRODEPOSIZIONE è stata sviluppata alla Stanford University -> le molecole di DNA preconfezionate (cloni di DNA genomico, di c. DNA, prodotti di PCR oppure oligonucleotidi) sono depositati sul vetro usando strumenti meccanici per la deposizione. Il DNA è caricato per capillarità su un ago e piccole quantità di DNA sono rilasciate sulla superficie del vetro quando l’ago tocca la superficie. L’ago è lavato, carica il DNA successivo e lo deposita in posizione adiacente. La produzione veloce di microarray è resa possibile da una testa motorizzata robottizzata con molti aghi. I microarray possono contenere 10000 -100000 molecole di DNA in un’area piccolissima di 3, 6 cm 2. Gli aghi depositano una goccia del DNA sul supporto vetrino Gli aghi si spostano in un’ altra posizione, dopo il lavaggio

Microarrays di oligonucleotidi Questo tipo di array si ottiene sia per microdeposizione di gocce di oligonucleotidi sul supporto, sia con la sintesi diretta di oligonucleotidi sul supporto; supporto si può raggiungere una densità di 100. 000 oligonucleotidi/per vetrino (da 20 a 60 basi). Offrono vantaggi rispetto ai microarray di c. DNA oppure di DNA genomico perché sono in grado di svelare SNPs e di distinguere quindi tra sequenze molto simili tra loro

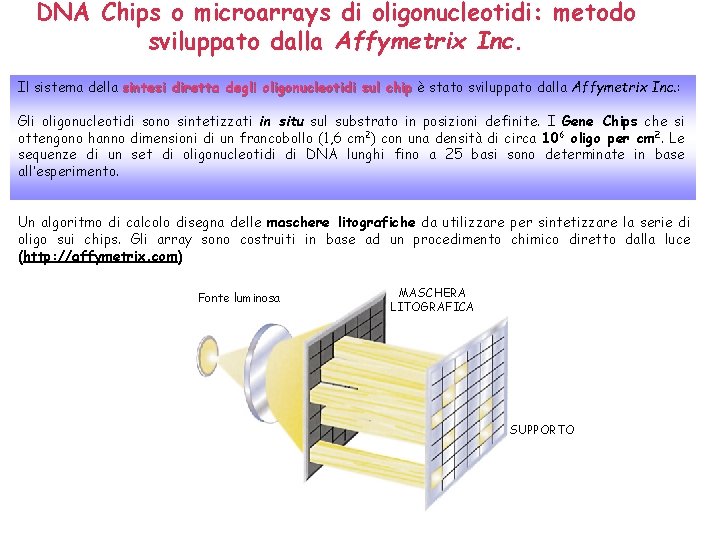
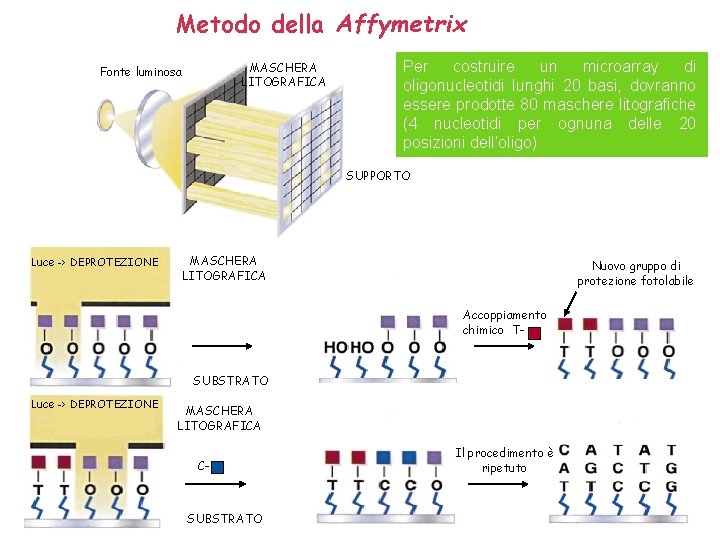
DNA Chips o microarrays di oligonucleotidi: metodo sviluppato dalla Affymetrix Inc. Il sistema della sintesi diretta degli oligonucleotidi sul chip è stato sviluppato dalla Affymetrix Inc. : Gli oligonucleotidi sono sintetizzati in situ sul substrato in posizioni definite. I Gene Chips che si ottengono hanno dimensioni di un francobollo (1, 6 cm 2) con una densità di circa 106 oligo per cm 2. Le sequenze di un set di oligonucleotidi di DNA lunghi fino a 25 basi sono determinate in base all’esperimento. Un algoritmo di calcolo disegna delle maschere litografiche da utilizzare per sintetizzare la serie di oligo sui chips. Gli array sono costruiti in base ad un procedimento chimico diretto dalla luce (http: //affymetrix. com) Fonte luminosa MASCHERA LITOGRAFICA SUPPORTO

Metodo della Affymetrix MASCHERA LITOGRAFICA Fonte luminosa Per costruire un microarray di oligonucleotidi lunghi 20 basi, dovranno essere prodotte 80 maschere litografiche (4 nucleotidi per ognuna delle 20 posizioni dell’oligo) SUPPORTO Luce -> DEPROTEZIONE MASCHERA LITOGRAFICA Nuovo gruppo di protezione fotolabile Accoppiamento chimico T- SUBSTRATO Luce -> DEPROTEZIONE MASCHERA LITOGRAFICA C- SUBSTRATO Il procedimento è ripetuto

Schema di esperimento basato sui microarray Un tipico esperimento che utilizzi i microarray comprende cinque fasi principali: 1. deposizione delle sonde sul supporto rigido; ogni singolo vetrino può contenere da 5000 a 40000 prodotti di amplificazione o c. DNA oppure OLIGONUCLEOTIDI. 2. preparazione del materiale genetico da analizzare per esempio una miscela di c. DNA che viene marcata con molecole fluorescenti (fluorocromi) 3. ibridazione dei campioni fluorescenti sul microarray 4. lettura dei valori di fluorescenza, effettuata tramite apposito scanner; si valuta il quadro di fluorescenza e i risultati sono elaborati da un computer. Il livello di fluorescenza in ogni singola goccia di DNA è proporzionale ai livelli di espressione genica. Si possono usare sullo STESSO MICROARRAY due c. DNA preparati da cellule diverse e marcati con coloranti fluorescenti diversi. Si ottiene come risposta una mappa a colori che definisce un profilo di espressione, che consente di confrontare i quadri di espressione genica in tessuti diversi o nello stesso tessuto in differenti condizioni oppure in cellule a stadi diversi di sviluppo

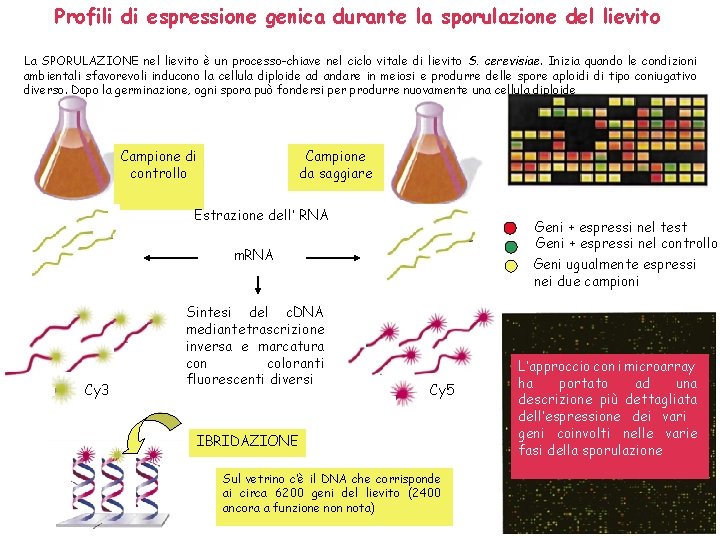
Profili di espressione genica durante la sporulazione del lievito La SPORULAZIONE nel lievito è un processo-chiave nel ciclo vitale di lievito S. cerevisiae. Inizia quando le condizioni ambientali sfavorevoli inducono la cellula diploide ad andare in meiosi e produrre delle spore aploidi di tipo coniugativo diverso. Dopo la germinazione, ogni spora può fondersi per produrre nuovamente una cellula diploide Campione da saggiare Campione di controllo Estrazione dell’ RNA Geni + espressi nel test Geni + espressi nel controllo Geni ugualmente espressi nei due campioni m. RNA Cy 3 Sintesi del c. DNA mediantetrascrizione inversa e marcatura con coloranti fluorescenti diversi Cy 5 IBRIDAZIONE Sul vetrino c’è il DNA che corrisponde ai circa 6200 geni del lievito (2400 ancora a funzione non nota) L’approccio con i microarray ha portato ad una descrizione più dettagliata dell’espressione dei vari geni coinvolti nelle varie fasi della sporulazione