Clonage Molculaire Dfinitions q Clonage r Obtenir un

Clonage Moléculaire

Définitions q Clonage : r Obtenir un morceau d’ADN à partir de la source originale (Génome) et l’introduire dans un vecteur d’ADN q Sous-clonage: r Transfère d’une insertion d’ADN cloné ou d’une partie de celle-ci d’un vecteur à un autre vecteur q Plasmide recombinant: r Vecteur dans lequel un ADN étranger a été introduit q Organisme recombinant r Organisme dans lequel un vecteur recombinant a été introduit

Pourquoi cloner? q Séparer, identifier, manipuler ou exprimer un fragment spécifique d’ADN 3

Étape 1 - Séparer q Deux approches: q Fragmenter/digérer l’ADN génomique q Génère un très grand nombre de fragments q Peut-être difficile de retrouver le fragment d’intérêt q Amplification q Beaucoup par PCR moins de fragments q Beaucoup plus facile de retrouver la séquence d’intérêt

Réplication & Amplification d’ADN La Réaction de la Polymérase en Chaîne
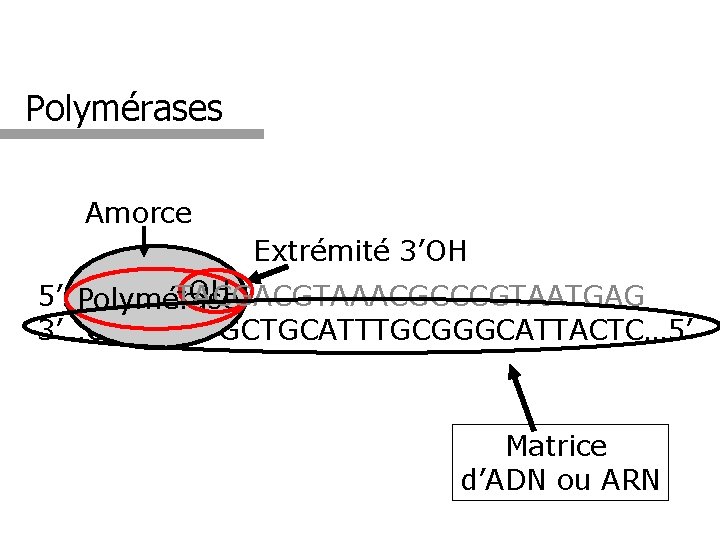
Polymérases Amorce Extrémité 3’OH -OH 5’…GTACT TACGACGTAAACGCCCGTAATGAG Polymérase 3’…CATGAATGCTGCATTTGCGGGCATTACTC… 5’ Matrice d’ADN ou ARN

La Réaction de la Polymérase en Chaîne q Réplication répétitive d’une région donnée d’ADN q Permet l’amplification exponentielle d’une région donnée d’ADN q Augmente la représentation relative d’une région d’intérêt q Permet l’isolation d’une région donnée d’ADN 7
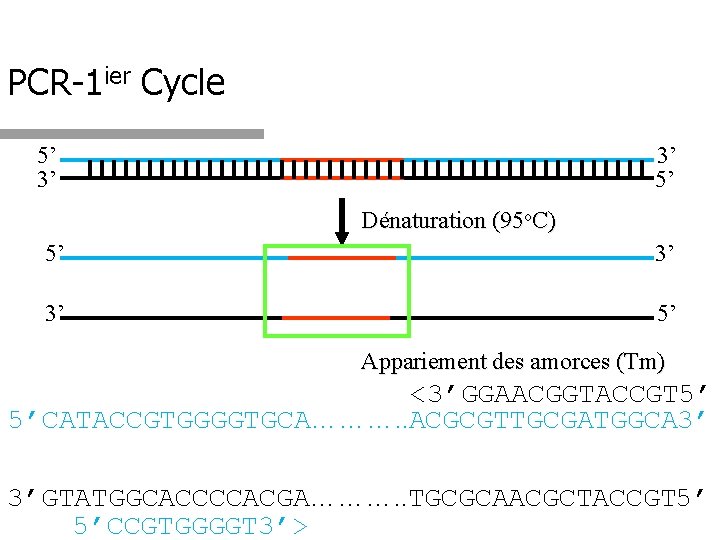
PCR-1 ier Cycle 5’ 3’ 3’ 5’ Dénaturation (95 o. C) 5’ 3’ 3’ 5’ Appariement des amorces (Tm) <3’GGAACGGTACCGT 5’ 5’CATACCGTGGGGTGCA………. . ACGCGTTGCGATGGCA 3’ 3’GTATGGCACCCCACGA………. . TGCGCAACGCTACCGT 5’ 5’CCGTGGGGT 3’>
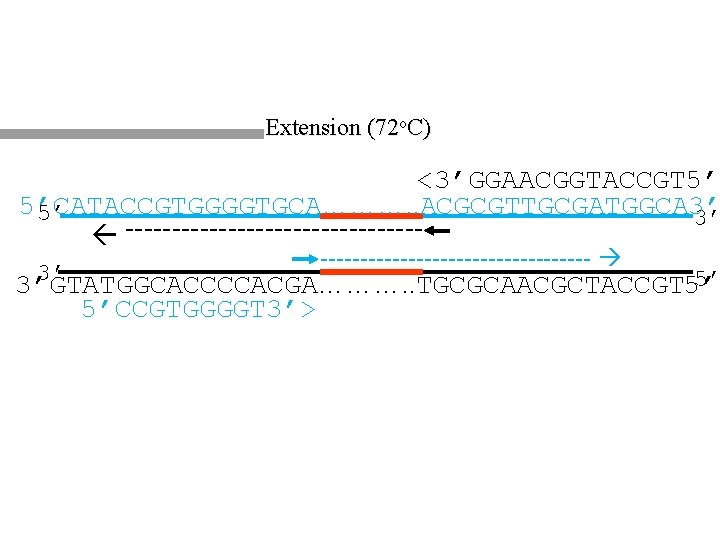
Extension (72 o. C) <3’GGAACGGTACCGT 5’ 5’CATACCGTGGGGTGCA………. . ACGCGTTGCGATGGCA 3’ 5’ 3’ ----------------- 3’ 5’ 3’GTATGGCACCCCACGA………. . TGCGCAACGCTACCGT 5’ 5’CCGTGGGGT 3’> 9



Problème q Vous souhaitez amplifier une séquence de 1 kb à partir de 10 ng d’une matrice simple brin de 10 kb avec des amorces couvrant les positions 12 -37 et 10071037. Combien de cycles faut-il pour obtenir 1µg du produit désiré?

Solution q Déterminer la masse initiale du produit désiré q q 10 kb = 10 ng donc 1 kb = 1 ng ou 10 -3µg (Simple brin) q Double brin serait 2 X 10 -3 µg Déterminer le nombre de cycles à partir de la masse initiale du produit désiré q q Déterminer le nombre de cycles afin d’obtenir le produit double brin désiré q q 1µg = 2 X 10 -3µg(2 n); résoudre pour n – Approx. 9 3 cycles Total: 9+3 = 12

Survol des Cycles du PCR q Amorces: q Courte séquence nucléotidiques simple brins complémentaires aux cibles q 15 -30 nucléotides q Utilisée en excès comparativement à la cible afin de favoriser l’appariement des amorces plutôt que l’appariement des matrices

Survol des Cycles du PCR q Appariement: Température à laquelle les amorces s’apparient aux séquences complémentaires q Dois être sous le Tm des amorces q Dois être une température qui permet aux deux amorces de s’apparier q Habituellement entre 55 -75 o. C q q Extension: Fait à la température optimale pour la polymérase ADN q Habituellement 72 -75 o. C pour la polymérase Taq q

Amorces q Caractéristiques: q Courts oligonucléotides complémentaires aux séquences qui bordent la région d’intérêt q Établis le point d’initiation de la réplication q Établis le point de terminaison de la réplication 16
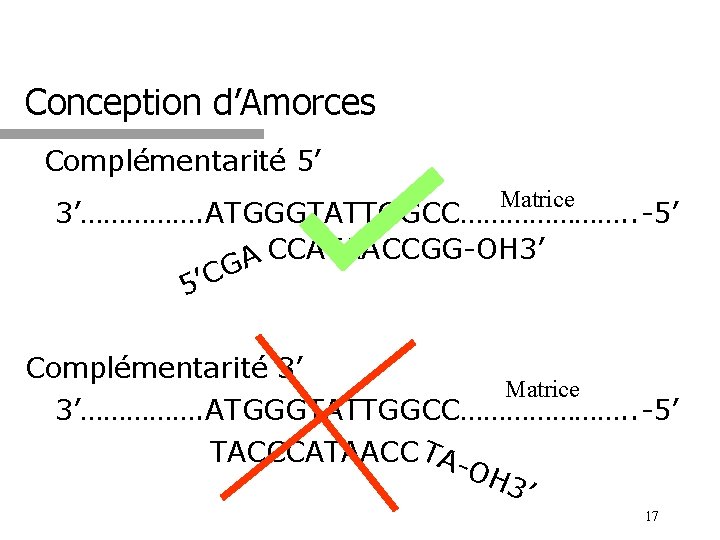
Conception d’Amorces Complémentarité 5’ Matrice 3’……………. ATGGGTATTGGCC…………………. . -5’ CCATAACCGG-OH 3’ A G C ’ 5 Complémentarité 3’ Matrice 3’……………. ATGGGTATTGGCC…………………. . -5’ TACCCATAACC TAOH 3’ 17
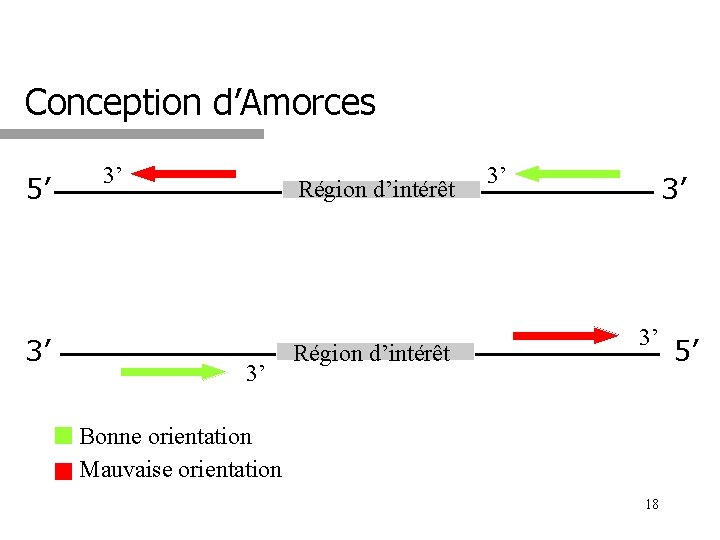
Conception d’Amorces 5’ 3’ 3’ Région d’intérêt 3’ 3’ 3’ Bonne orientation Mauvaise orientation 18 5’

Amorces 2 amorces sont requises pour une amplification exponentielle q Amorce « Forward » q q q Amorce « Reverse » q q Amorce dont la séquence est la même que celle de la matrice indiquée Amorce dont la séquence est complémentaire à celle de la matrice indiquée Exemple 3’-GCGGTT • • • • • ATCGTTA-5’ q q Amorce « Forward » : ATTGCTA Amorce « Reverse » : CGCCAA

Problème 5’-AAAAAA GGGGGGG-3’ q Vous désirez amplifier la séquence représentée par la boite. Quelle paire d’amorces est dans la bonne orientation pour accomplir ceci? 1234 - AAAAAA TTTTTT GGGGGG CCCCCC 20

Utilité le la PCR q Amplification et isolation d’une région donnée en changeant sa représentation relative q Entre 100 pb et 10 Kpb q Criblage pour déterminer la présence d’une séquence d’intérêt q Présence ou absence d’un produit d’amplification q Mutagenèse q dirigée Utilisé pour ajouter ou enlever des nucléotides sur la matrice originale 21
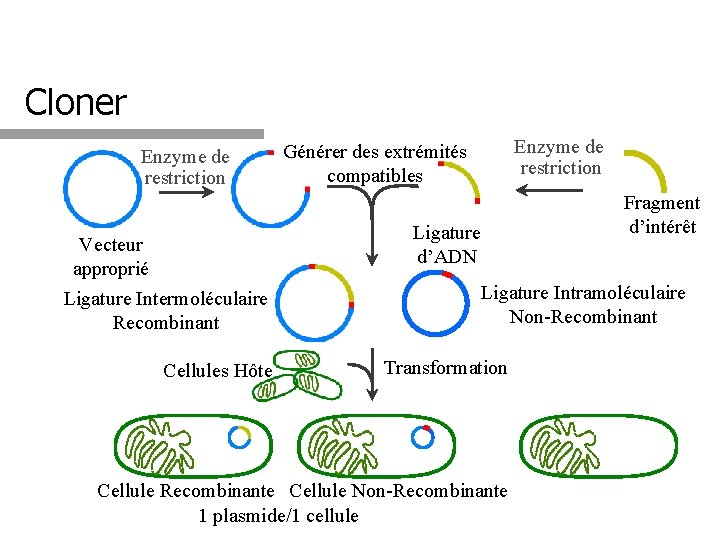
Cloner Enzyme de restriction Générer des extrémités compatibles Fragment d’intérêt Ligature d’ADN Vecteur approprié Ligature Intermoléculaire Recombinant Cellules Hôte Ligature Intramoléculaire Non-Recombinant Transformation Cellule Recombinante Cellule Non-Recombinante 1 plasmide/1 cellule
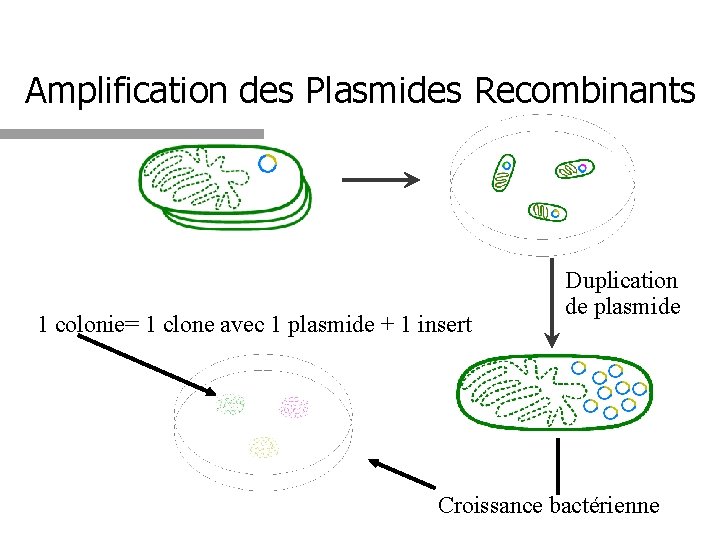
Amplification des Plasmides Recombinants 1 colonie= 1 clone avec 1 plasmide + 1 insert Duplication de plasmide Croissance bactérienne

Criblage et Identification de Clones Recombinants Plasmidiques q Cartographie q PCR de restriction
- Slides: 24