CIDOS NUCLICOS Nucleotdeos estrutura geral Base nitrogenada P

ÁCIDOS NUCLÉICOS
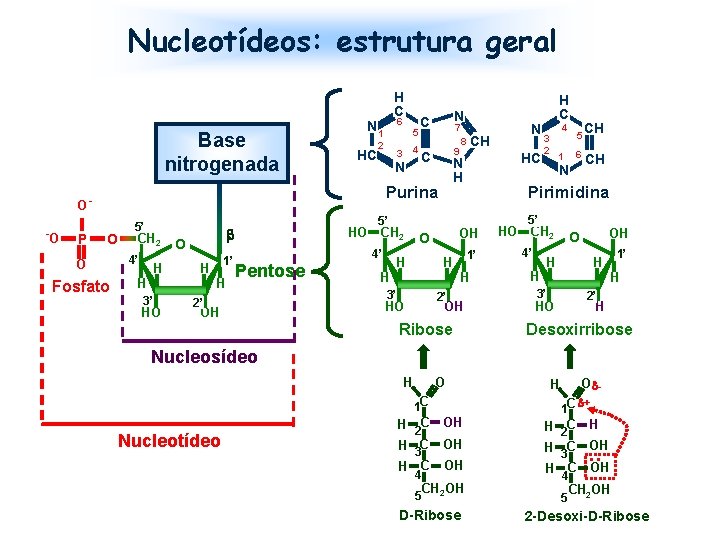
Nucleotídeos: estrutura geral Base nitrogenada P 6 N 1 HC 2 5 4 3 N N C 7 O O Fosfato 5’ CH 2 4’ H O 1’ H H H 3’ HO 4’ Pentose 2’ OH O H 3’ 4 3 2 N 4’ Ribose CH CH 5’ 1’ OH 6 1 HO CH 2 2’ 5 Pirimidina H HO H C OH H H N HC N H 5’ HO CH 2 CH 8 9 C Purina O- -O H C OH O H 1’ H H H 3’ 2’ HO H Desoxirribose Nucleosídeo O H 1 C Nucleotídeo H 2 C H C OH H C 3 4 O - H 1 C + H OH H 2 C H C OH CH 2 OH 5 D-Ribose 3 4 OH • • CH 2 OH 5 2 -Desoxi-D-Ribose
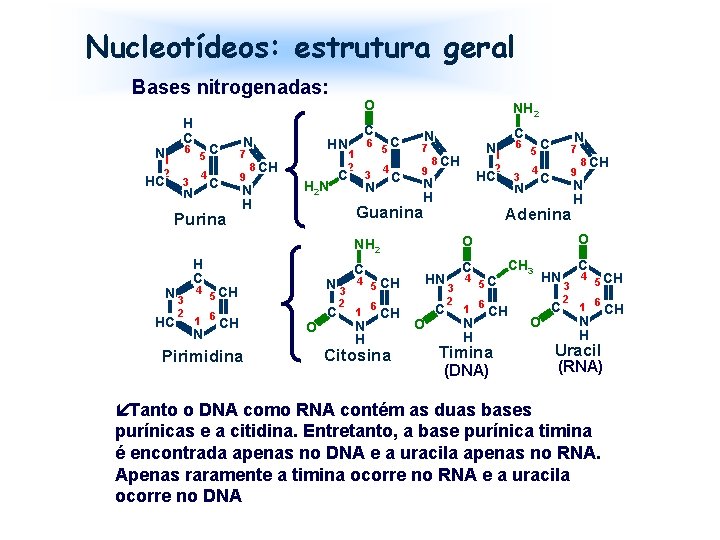
Nucleotídeos: estrutura geral Bases nitrogenadas: H C C 5 6 N 1 2 HC 3 4 N C Purina N 3 HC 2 N 7 9 HN 8 CH N H H 2 N N 3 4 5 CH N Pirimidina C C 6 1 2 3 N NH 2 N C 5 7 4 9 C 8 CH O C 2 HC N H C C N H 6 CH Citosina HN O 3 5 4 N N C 7 9 C Adenina O 1 6 2 NH 2 4 5 CH C N 1 Guanina H C 1 6 CH O C 3 2 4 5 C Timina (DNA) N H O CH 3 1 6 CH N H 8 CH HN O C C 3 2 4 5 CH 1 6 CH N H Uracil (RNA) íTanto o DNA como RNA contém as duas bases purínicas e a citidina. Entretanto, a base purínica timina é encontrada apenas no DNA e a uracila apenas no RNA. Apenas raramente a timina ocorre no RNA e a uracila ocorre no DNA
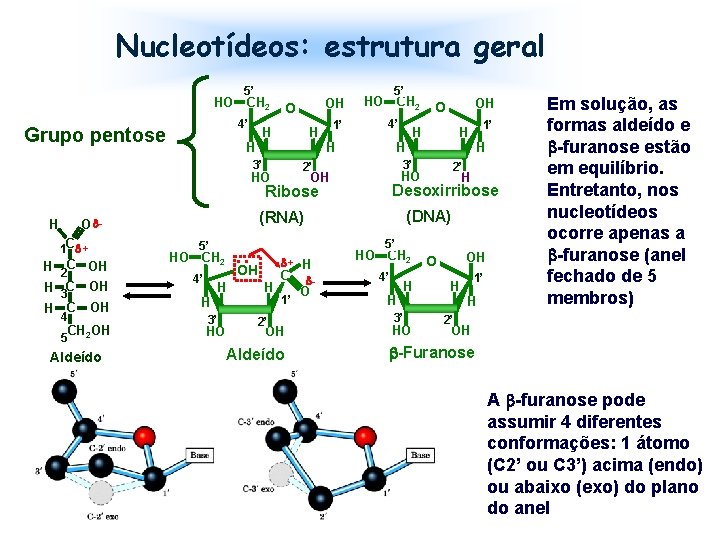
Nucleotídeos: estrutura geral 5’ HO CH 2 4’ Grupo pentose O H OH 1’ 4’ H H 5’ HO CH 2 3’ 1 C + H C 4 OH CH 2 OH 5 Aldeído HO CH 2 • • OH 4’ H H H 3’ HO 2’ H Desoxirribose (DNA) 5’ 5’ H 2 C OH H 3 C OH H HO OH (RNA) O - + H C 1’ 2’ OH Aldeído O 1’ H 3’ 2’ Ribose H H HO OH O HO CH 2 4’ H OH O H 3’ HO 1’ H H Em solução, as formas aldeído e -furanose estão em equilíbrio. Entretanto, nos nucleotídeos ocorre apenas a -furanose (anel fechado de 5 membros) 2’ OH -Furanose A -furanose pode assumir 4 diferentes conformações: 1 átomo (C 2’ ou C 3’) acima (endo) ou abaixo (exo) do plano do anel
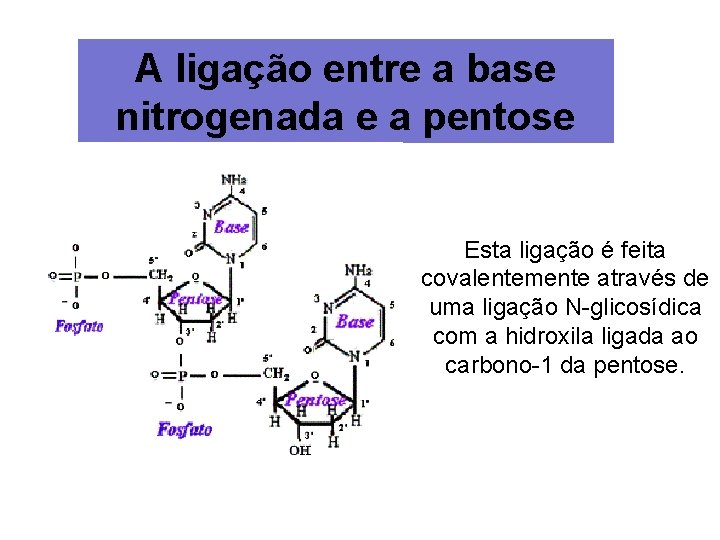
A ligação entre a base nitrogenada e a pentose Esta ligação é feita covalentemente através de uma ligação N-glicosídica com a hidroxila ligada ao carbono-1 da pentose.
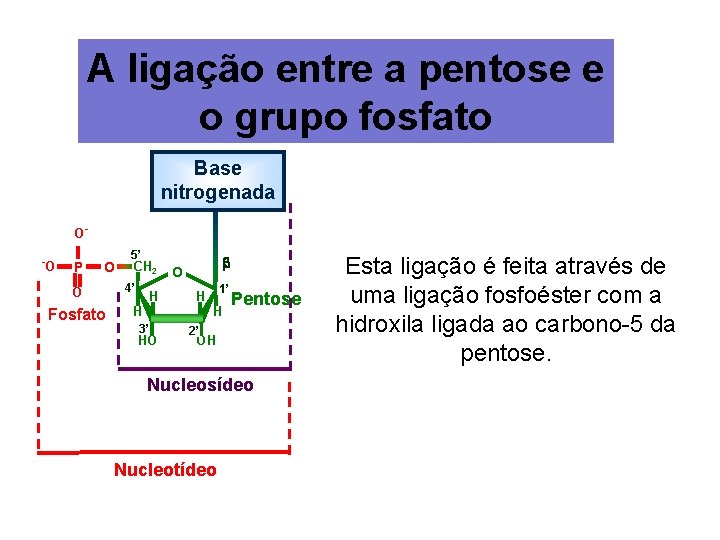
A ligação entre a pentose e o grupo fosfato Base nitrogenada O- -O P O O Fosfato 5’ CH 2 4’ H O 1’ H H H 3’ HO Pentose 2’ OH Nucleosídeo Nucleotídeo Esta ligação é feita através de uma ligação fosfoéster com a hidroxila ligada ao carbono-5 da pentose.
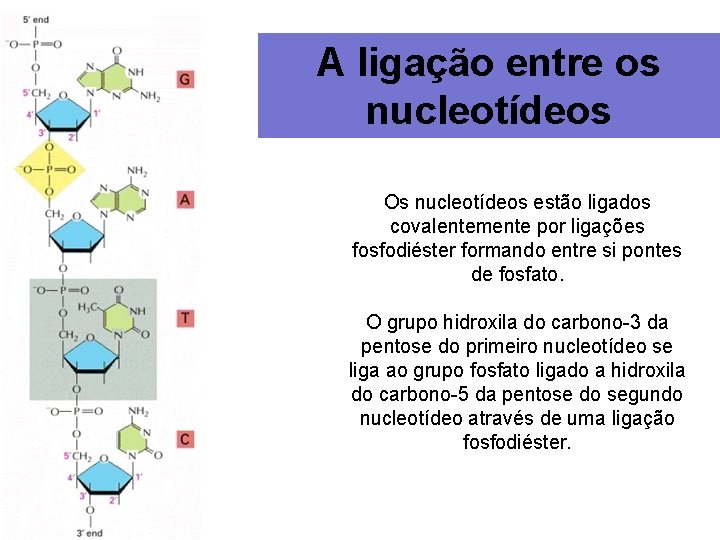
A ligação entre os nucleotídeos Os nucleotídeos estão ligados covalentemente por ligações fosfodiéster formando entre si pontes de fosfato. O grupo hidroxila do carbono-3 da pentose do primeiro nucleotídeo se liga ao grupo fosfato ligado a hidroxila do carbono-5 da pentose do segundo nucleotídeo através de uma ligação fosfodiéster.
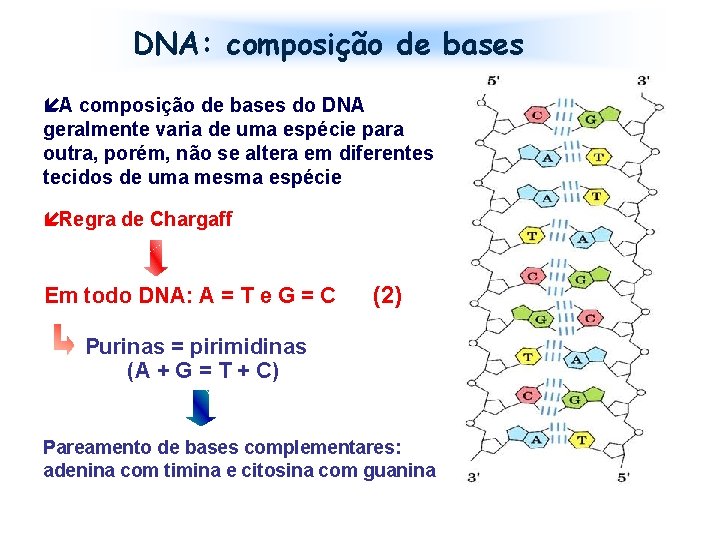
DNA: composição de bases íA composição de bases do DNA geralmente varia de uma espécie para outra, porém, não se altera em diferentes tecidos de uma mesma espécie íRegra de Chargaff Em todo DNA: A = T e G = C (2) Purinas = pirimidinas (A + G = T + C) Pareamento de bases complementares: adenina com timina e citosina com guanina

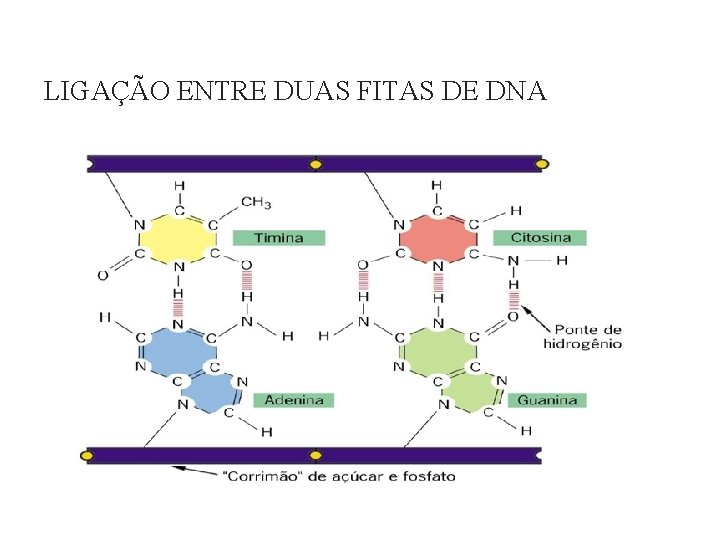
LIGAÇÃO ENTRE BASES NITROGENADAS A ligação feita por pontes de hidrogênio: Timina (T) liga-se à Adenina (A) - duas pontes de hidrogênio; Citosina (C) liga-se à Guanina (G) - três pontes de hidrogênio.

LIGAÇÃO ENTRE BASES NITROGENADAS Tais pontes de hidrogênio são formadas em decorrência da presença de grupos ceto (C=O) e amino (C-NH 2) nas bases; Te. U ceto e amino G grupo ceto e amino A amino C grupo ceto e amino
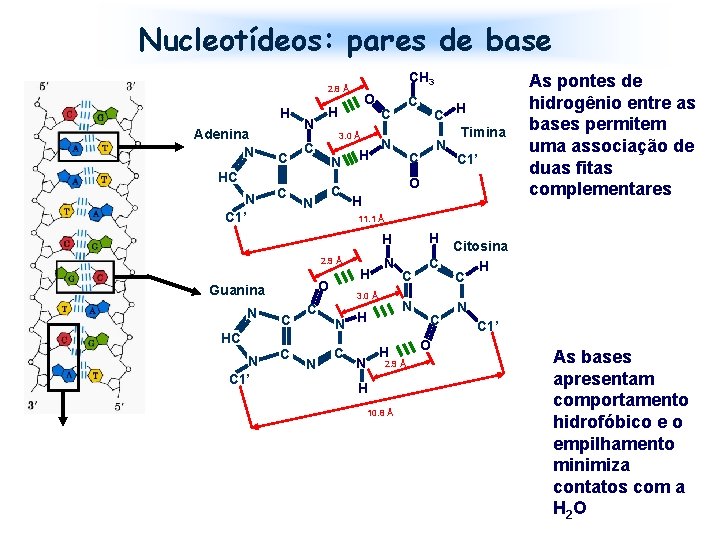
Nucleotídeos: pares de base CH 3 2. 8 Å H Adenina N C N H C N C 1’ N C C 3. 0 Å HC C O H N C H Timina C 1’ O H As pontes de hidrogênio entre as bases permitem uma associação de duas fitas complementares 11. 1 Å H H 2. 9 Å H O Guanina N C 1’ C C HC N N 3. 0 Å N C N H H N C 2. 9 Å H 10. 8 Å Citosina C H C C O N C 1’ As bases apresentam comportamento hidrofóbico e o empilhamento minimiza contatos com a H 2 O
LIGAÇÃO ENTRE BASES NITROGENADAS Pirimidina < Purina Logo, AT e CG tem, aproximadamente, o mesmo tamanho; Isso proporciona uma dimensão proporcional ao longo da molécula de DNA. Bases nitrogenadas: O H C C 5 6 N 1 2 HC 3 N 4 N 7 9 C Purina N 3 HC 2 H C 4 5 1 6 N 8 N H HN CH H 2 N C NH 2 C 1 2 6 5 4 3 N C C N 7 8 9 CH Guanina N 3 CH Pirimidina 2 HC N H O C 2 C CH HN 6 CH C N H 6 3 5 4 N N C 7 9 C Citosina O 4 5 C 1 6 N H CH 3 CH Timina (DNA) CH O C 3 2 8 N H O 4 5 1 C Adenina NH 2 CH N 1 HN O C C 3 2 5 CH 1 6 CH 4 N H Uracil (RNA)
LIGAÇÃO ENTRE DUAS FITAS DE DNA
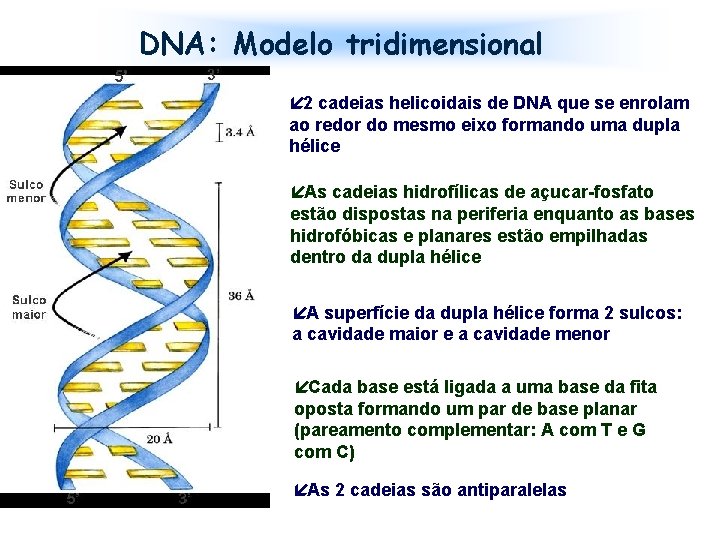
DNA: Modelo tridimensional í 2 cadeias helicoidais de DNA que se enrolam ao redor do mesmo eixo formando uma dupla hélice íAs cadeias hidrofílicas de açucar-fosfato estão dispostas na periferia enquanto as bases hidrofóbicas e planares estão empilhadas dentro da dupla hélice íA superfície da dupla hélice forma 2 sulcos: a cavidade maior e a cavidade menor íCada base está ligada a uma base da fita oposta formando um par de base planar (pareamento complementar: A com T e G com C) íAs 2 cadeias são antiparalelas
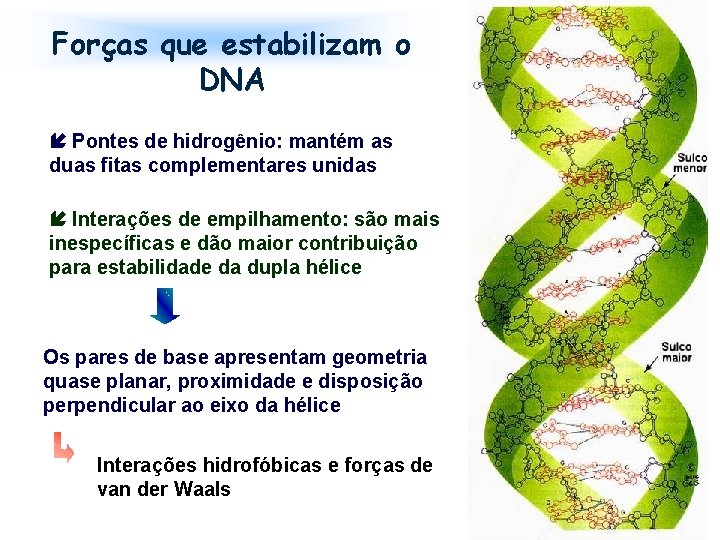
Forças que estabilizam o DNA Pontes de hidrogênio: mantém as duas fitas complementares unidas Interações de empilhamento: são mais inespecíficas e dão maior contribuição para estabilidade da dupla hélice Os pares de base apresentam geometria quase planar, proximidade e disposição perpendicular ao eixo da hélice Interações hidrofóbicas e forças de van der Waals

REFLEXÃO Qual a ligação mais difícil de ser quebrada? Adenina – Timina ou Guanina – Citosina? Se uma sequência de uma fita de polinucleotídeos fosse AATCCATGT, qual seria o filamento complementar?
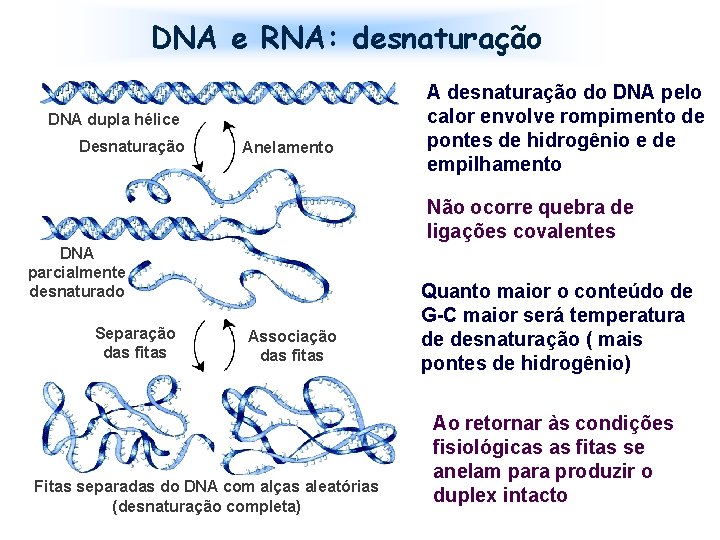
DNA e RNA: desnaturação DNA dupla hélice Desnaturação Anelamento A desnaturação do DNA pelo calor envolve rompimento de pontes de hidrogênio e de empilhamento Não ocorre quebra de ligações covalentes DNA parcialmente desnaturado Separação das fitas Associação das fitas Fitas separadas do DNA com alças aleatórias (desnaturação completa) Quanto maior o conteúdo de G-C maior será temperatura de desnaturação ( mais pontes de hidrogênio) Ao retornar às condições fisiológicas as fitas se anelam para produzir o duplex intacto
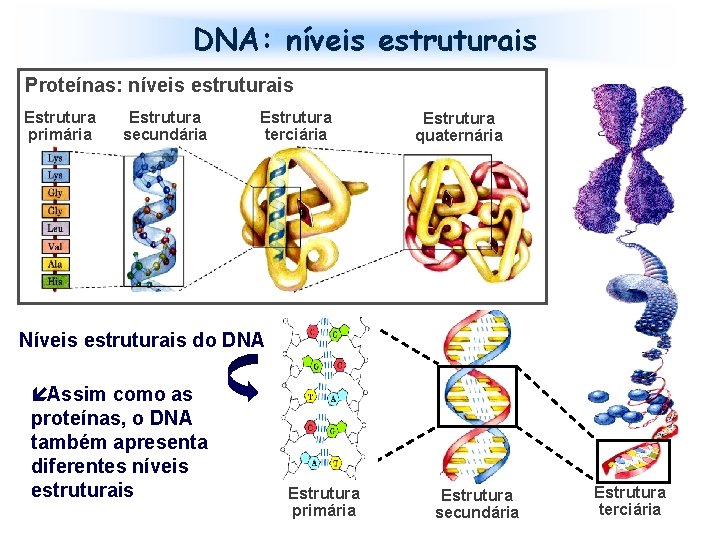
DNA: níveis estruturais Proteínas: níveis estruturais Estrutura primária Estrutura secundária Estrutura terciária Estrutura quaternária Níveis estruturais do DNA íAssim como as proteínas, o DNA também apresenta diferentes níveis estruturais Estrutura primária Estrutura secundária Estrutura terciária
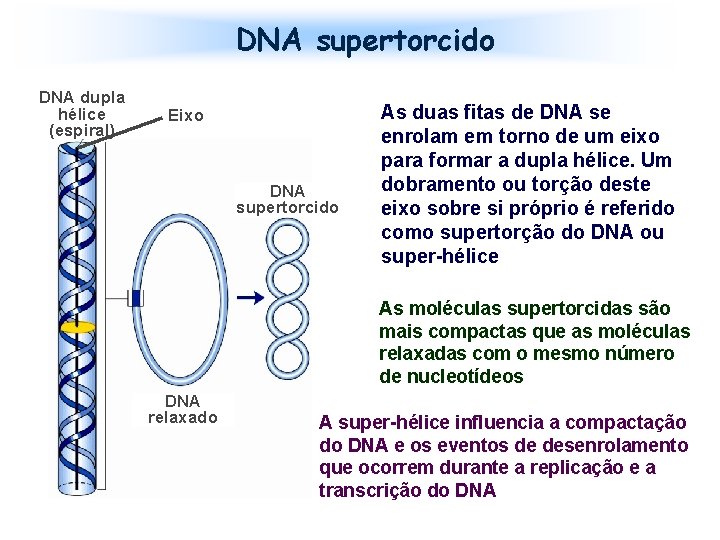
DNA supertorcido DNA dupla hélice (espiral) Eixo DNA supertorcido As duas fitas de DNA se enrolam em torno de um eixo para formar a dupla hélice. Um dobramento ou torção deste eixo sobre si próprio é referido como supertorção do DNA ou super-hélice As moléculas supertorcidas são mais compactas que as moléculas relaxadas com o mesmo número de nucleotídeos DNA relaxado A super-hélice influencia a compactação do DNA e os eventos de desenrolamento que ocorrem durante a replicação e a transcrição do DNA
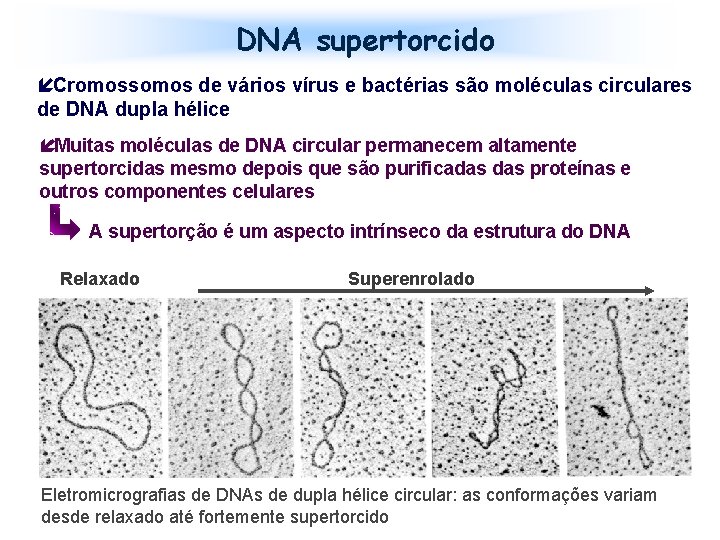
DNA supertorcido íCromossomos de vários vírus e bactérias são moléculas circulares de DNA dupla hélice íMuitas moléculas de DNA circular permanecem altamente supertorcidas mesmo depois que são purificadas proteínas e outros componentes celulares A supertorção é um aspecto intrínseco da estrutura do DNA Relaxado Superenrolado Eletromicrografias de DNAs de dupla hélice circular: as conformações variam desde relaxado até fortemente supertorcido
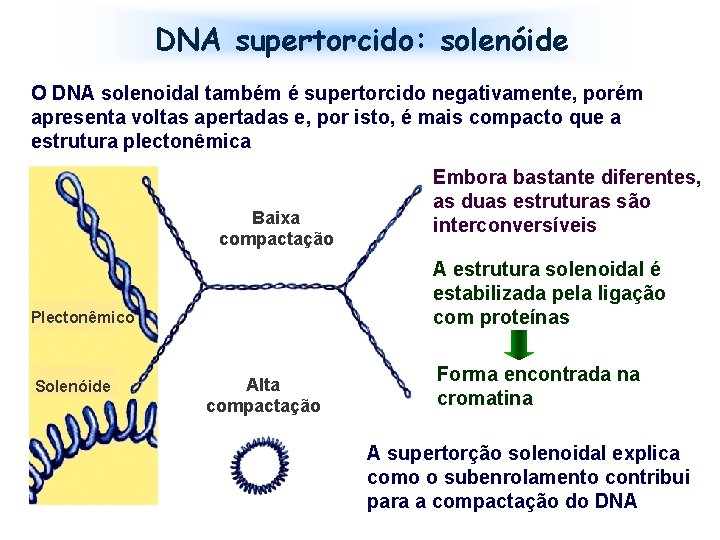
DNA supertorcido: solenóide O DNA solenoidal também é supertorcido negativamente, porém apresenta voltas apertadas e, por isto, é mais compacto que a estrutura plectonêmica Baixa compactação A estrutura solenoidal é estabilizada pela ligação com proteínas Plectonêmico Solenóide Embora bastante diferentes, as duas estruturas são interconversíveis Alta compactação Forma encontrada na cromatina A supertorção solenoidal explica como o subenrolamento contribui para a compactação do DNA
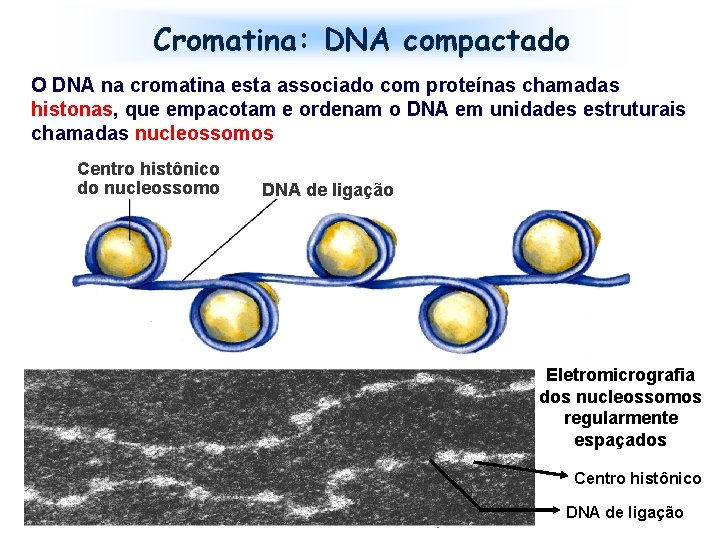
Cromatina: DNA compactado O DNA na cromatina esta associado com proteínas chamadas histonas, que empacotam e ordenam o DNA em unidades estruturais chamadas nucleossomos Centro histônico do nucleossomo DNA de ligação Eletromicrografia dos nucleossomos regularmente espaçados Centro histônico DNA de ligação
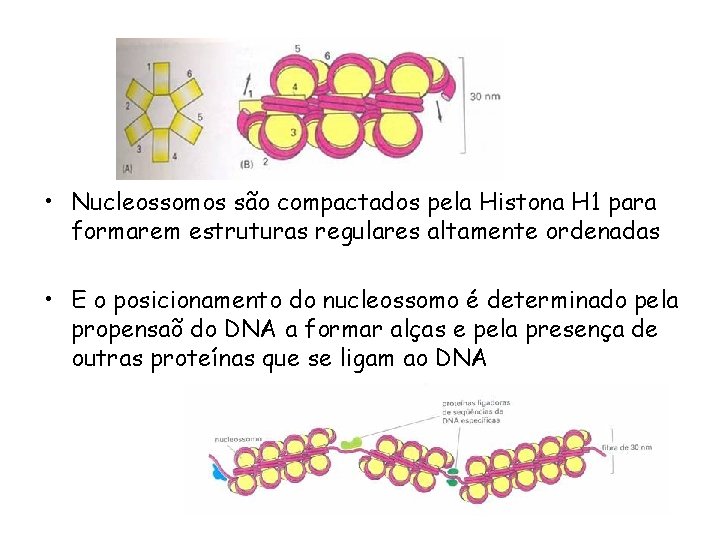
• Nucleossomos são compactados pela Histona H 1 para formarem estruturas regulares altamente ordenadas • E o posicionamento do nucleossomo é determinado pela propensaõ do DNA a formar alças e pela presença de outras proteínas que se ligam ao DNA
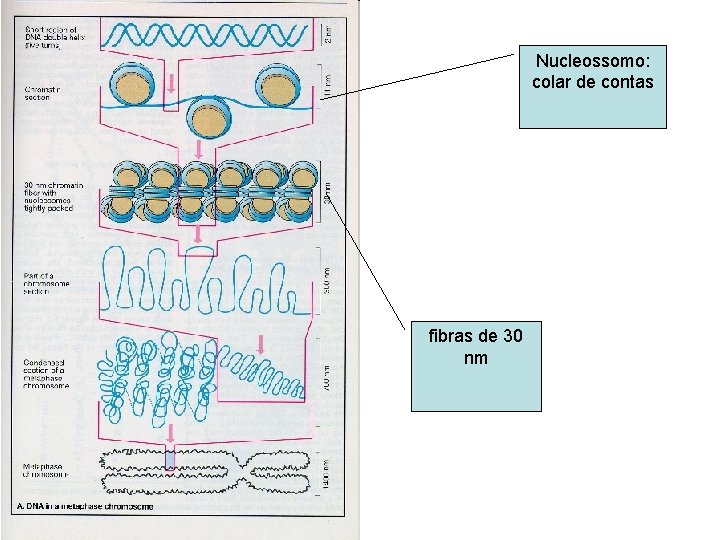
Nucleossomo: colar de contas fibras de 30 nm
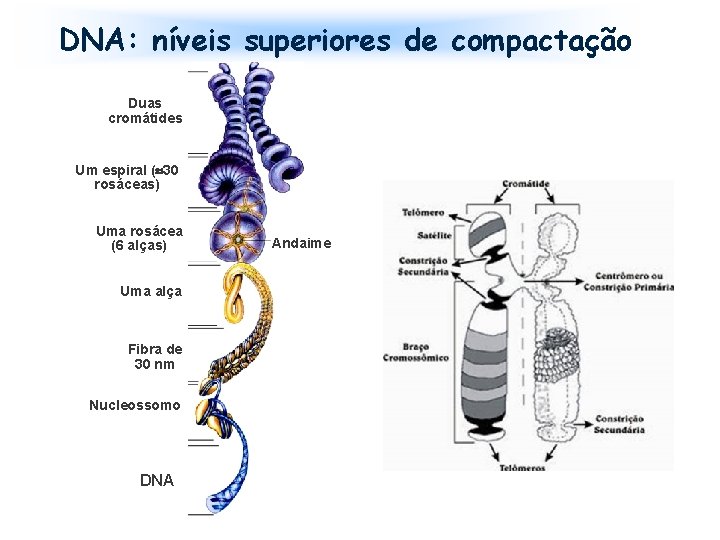
DNA: níveis superiores de compactação Duas cromátides Um espiral ( 30 rosáceas) Uma rosácea (6 alças) Uma alça Fibra de 30 nm Nucleossomo DNA Andaime
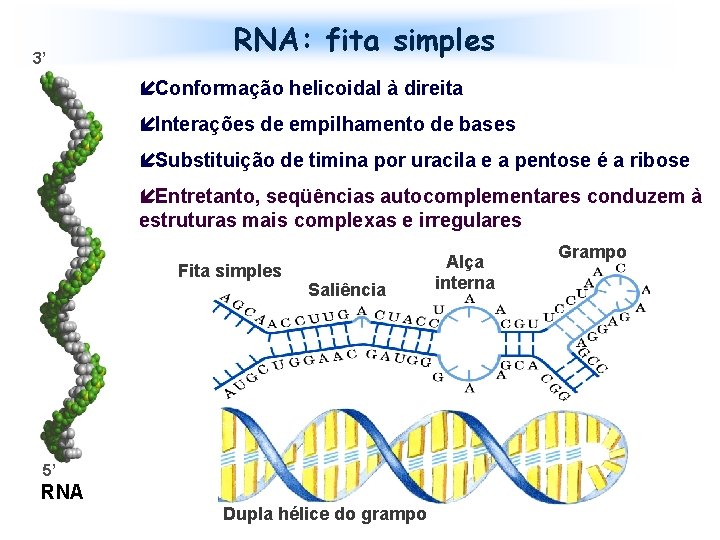
3’ RNA: fita simples íConformação helicoidal à direita íInterações de empilhamento de bases íSubstituição de timina por uracila e a pentose é a ribose íEntretanto, seqüências autocomplementares conduzem à estruturas mais complexas e irregulares Fita simples Saliência 5’ RNA Dupla hélice do grampo Alça interna Grampo
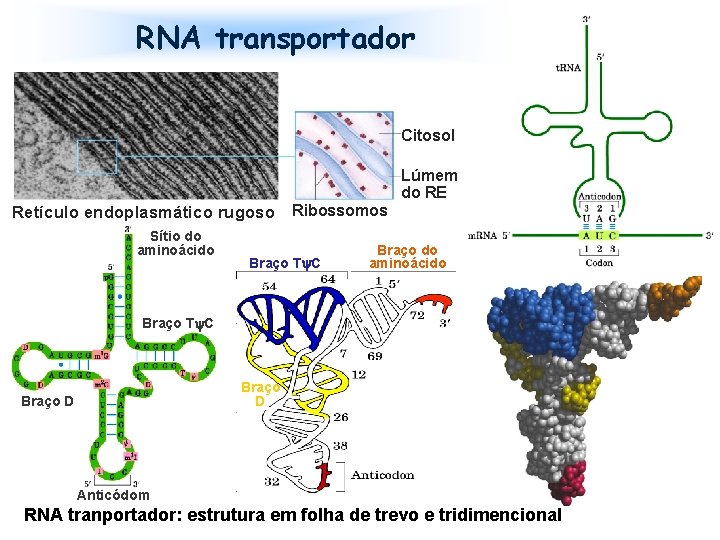
RNA transportador Citosol Lúmem do RE Retículo endoplasmático rugoso Ribossomos Sítio do aminoácido Braço T C Braço D Anticódom RNA tranportador: estrutura em folha de trevo e tridimencional
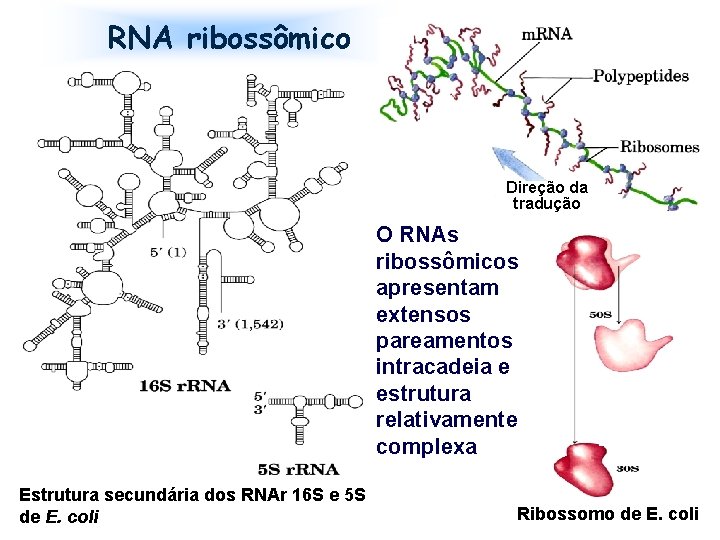
RNA ribossômico Direção da tradução O RNAs ribossômicos apresentam extensos pareamentos intracadeia e estrutura relativamente complexa Estrutura secundária dos RNAr 16 S e 5 S de E. coli Ribossomo de E. coli
- Slides: 28