Centro de Cincias Exatas e Natureza Departamento de















- Slides: 40

Centro de Ciências Exatas e Natureza Departamento de Biologia Molecular Disciplina: Genética Molecular Bases Moleculares da Regulação Gênica Aula: Generalidades Eleonidas Moura Lima

Sumário Organização do genoma procariótico Elementos de ação cis Elementos de ação trans Controle genético positivo Controle genético negativo Generalidades

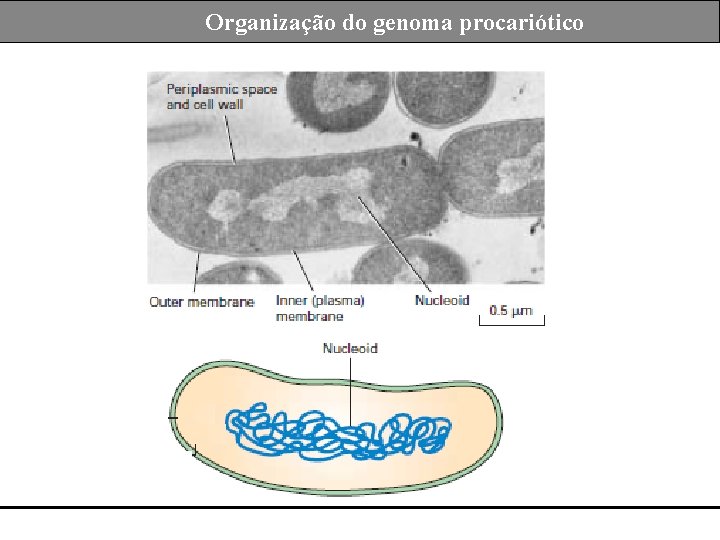
Sumário Organização do genoma procariótico

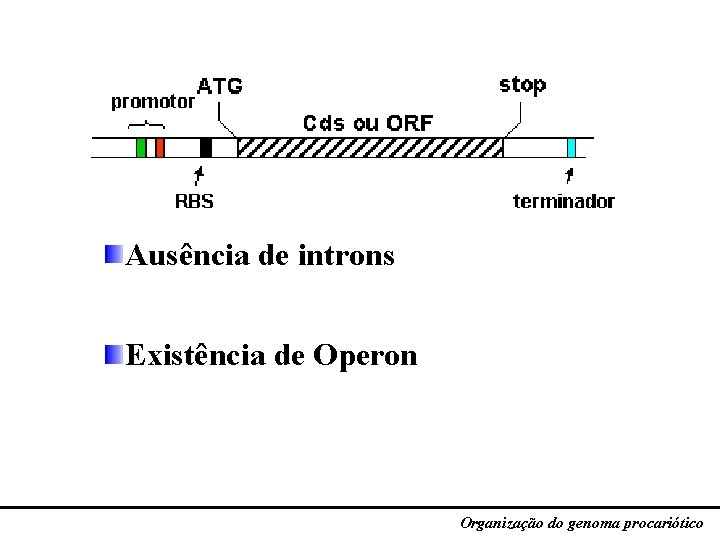
Sumário Ausência de introns Existência de Operon Organização do genoma procariótico

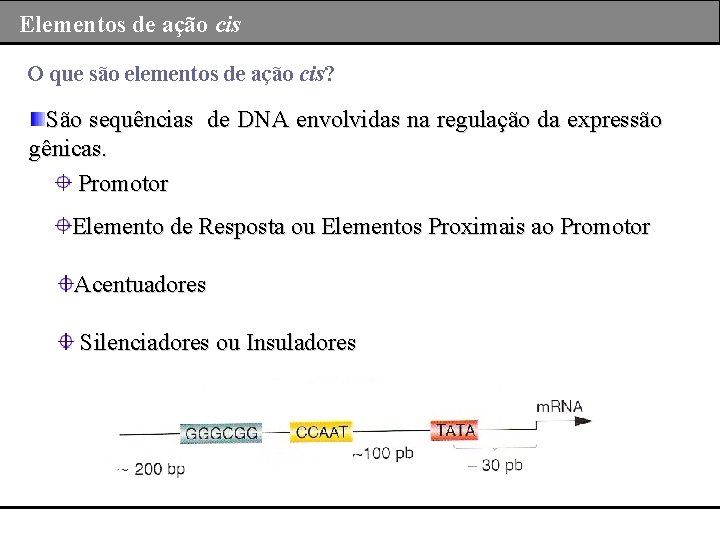
Elementos de ação cis O que são elementos de ação cis? São sequências de DNA envolvidas na regulação da expressão gênicas. Promotor Elemento de Resposta ou Elementos Proximais ao Promotor Acentuadores Silenciadores ou Insuladores

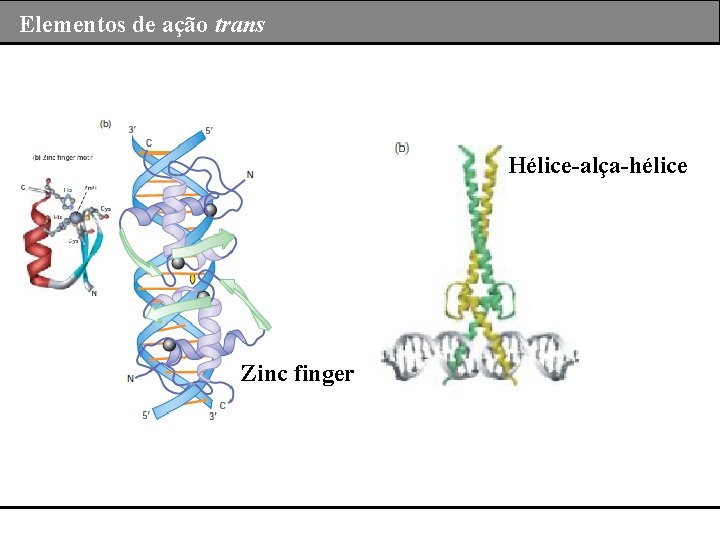
Elementos de ação trans O que são elementos de ação trans? São produto gênicos que possuem domínios de reconhecimento de sequência de ação cis (DNA) e domínio de interação proteína e estão envolvidos nos diferentes tipos de controle da expressão gênica. Ativadores Repressores Co-ativadores

Elementos de ação trans Hélice-alça-hélice Zinc finger

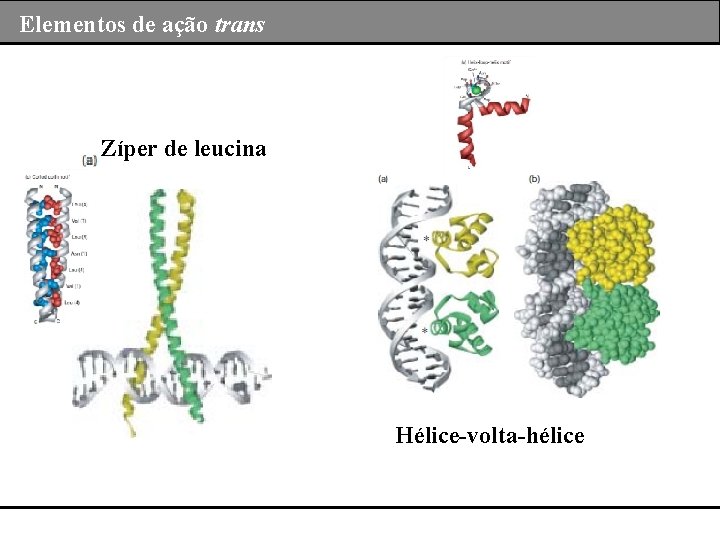
Elementos de ação trans Zíper de leucina Hélice-volta-hélice

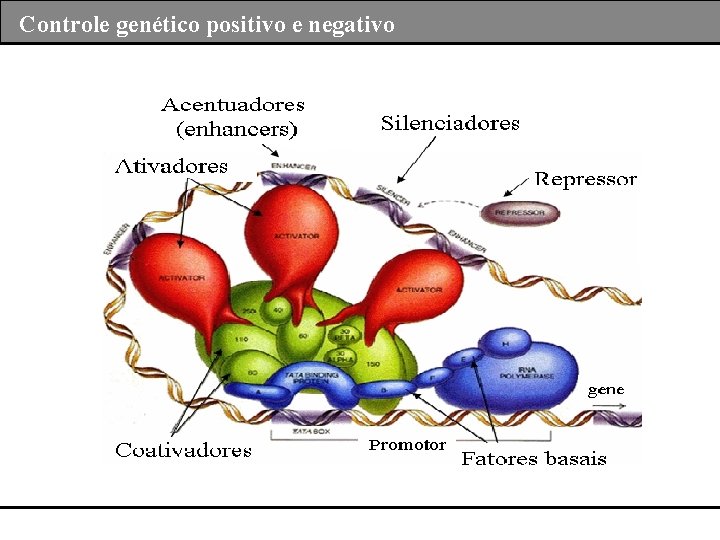
Controle genético positivo O controle positivo representação ativação da expressão gênicas através de interação combinatória entre ativadores, co-ativadores e elementos de ação cis (elementos proximais ao promotor e acentuadores).

Controle genético negativo O controle negativo é inativação da expressão gênicas através de interação combinatória entre repressores, ativadores, co-ativadores e elementos de ação cis (silenciadores)

Controle genético positivo e negativo

Centro de Ciências Exatas e Natureza Departamento de Biologia Molecular Disciplina: Genética Bases Moleculares da Regulação Gênica Aula: Regulação da expressão gênica em Procarioto Eleonidas Moura Lima

Sumário Níveis de regulação da expressão gênica em procariotos Tipos de controle da expressão O modelo Operon O operon lac O operon triptofano (trip) Atenuação da transcrição

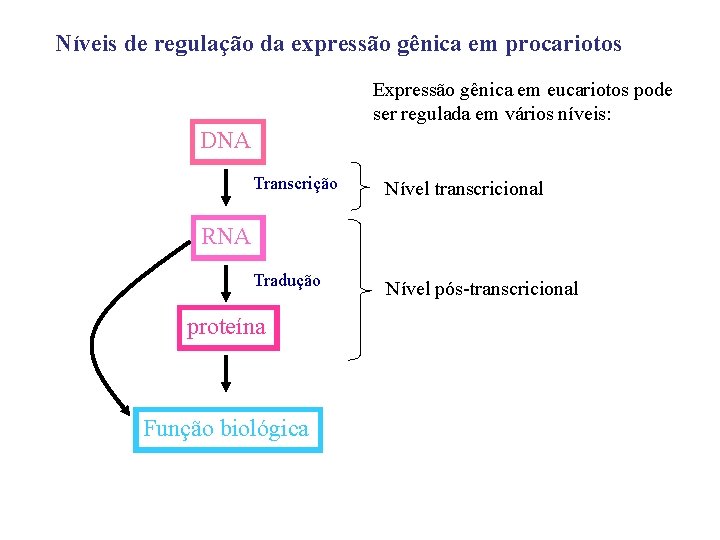
Níveis de regulação da expressão gênica em procariotos Expressão gênica em eucariotos pode ser regulada em vários níveis: DNA Transcrição Nível transcricional Tradução Nível pós-transcricional RNA proteína Função biológica

Estrutura da região promotora em E. coli Vários promotores em E. coli Sequências consenso -35 : TTGACA (reconhecida pela subunidade ) -10 : TATAAT – rica em AT, , mais fácil de abrir 1 a base (+1) : geralmente uma purina (A, G) • Estão separadas entre si por cerca de 15 -20 nucleotídios • Posição dá orientação ao promotor direciona RNA pol

Regulação da expressão gênica ao nível transcricional Os vários mecanismos regulatórios caem em duas categorias : • Liga/desliga a expressão gênica em resposta a alterações ambientais – mais importantes em procariotos • Circuitos pré-programados ou cascatas de expressão gênica : evento transcrição Genes A, B, C transcrição Genes D, E, F transcrição Assim por diante. . .

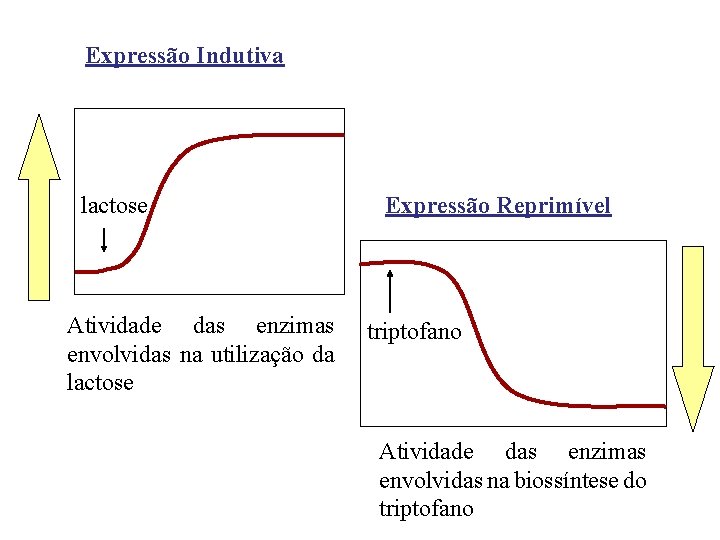
Tipos de expressão : a expressão dos genes pode ser 1) Constitutiva : o produto dos genes constitutivos (housekeeping) é sempre necessário Ex. : RNAt, RNAr, subunidades da RNA polimerase 2) Regulada : o produto do gene é necessário sob certas condições ambientais. Pode ser : ü Indutiva : uma molécula induz a expressão do gene (indutora) ü Reprimível : uma molécula reprime a expressão do gene (co -repressora)

Expressão Indutiva lactose Atividade das enzimas envolvidas na utilização da lactose Expressão Reprimível triptofano Atividade das enzimas envolvidas na biossíntese do triptofano

Tipos de controle da expressão : o controle pode ser negativo ou positivo O controle da expressão é feito por uma proteína reguladora, que é produto de um gene regulador Controle negativo Controle positivo Proteína reguladora desliga a expressão do gene Proteína reguladora liga a expressão do gene REPRESSORA ATIVADORA

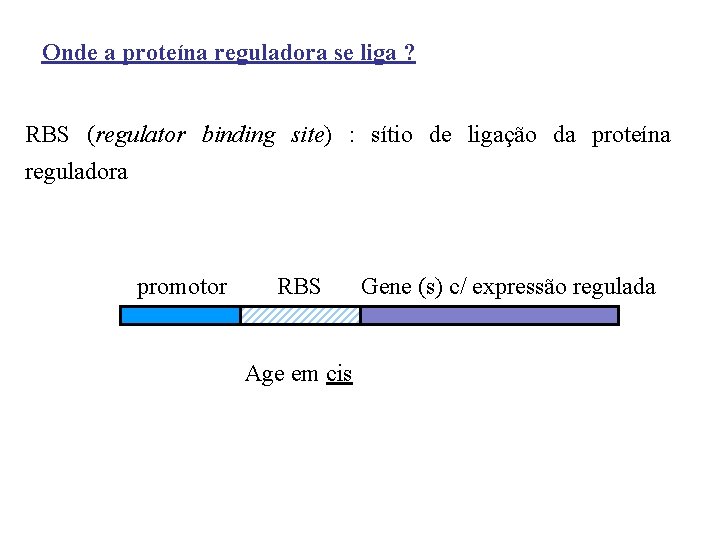
Onde a proteína reguladora se liga ? RBS (regulator binding site) : sítio de ligação da proteína reguladora promotor RBS Age em cis Gene (s) c/ expressão regulada

Região Promotora

Resumindo : participam do controle da expressão ü Indutor : molécula que induz a expressão de genes ü Co-repressora : molécula que reprime a expressão de genes ambiente ü Ativadores : produto de gene regulador que liga a expressão de um gene ü Repressores : produto de um gene regulador que desliga a expressão de um gene ü RBS : sítio adjacente ao promotor, ao qual o ativador ou o repressor se liga

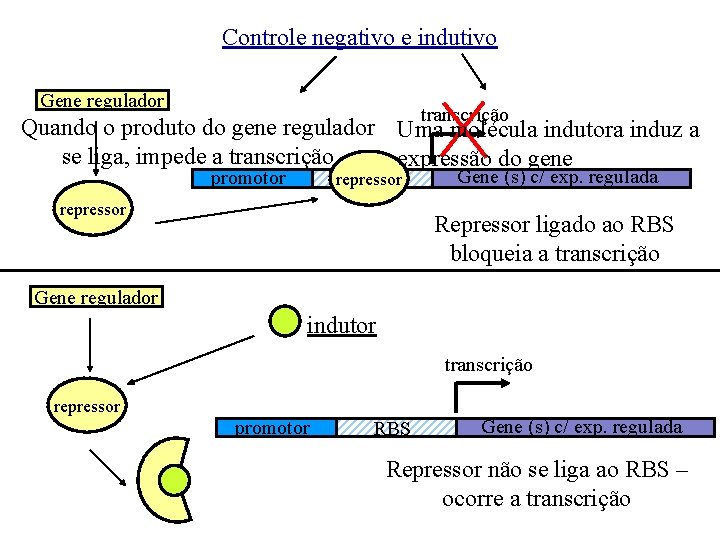
Controle negativo e indutivo Gene regulador transcrição Quando o produto do gene regulador Uma molécula indutora induz a se liga, impede a transcrição expressão do gene promotor repressor RBS repressor Gene (s) c/ exp. regulada Repressor ligado ao RBS bloqueia a transcrição Gene regulador indutor transcrição repressor promotor RBS Gene (s) c/ exp. regulada Repressor não se liga ao RBS – ocorre a transcrição

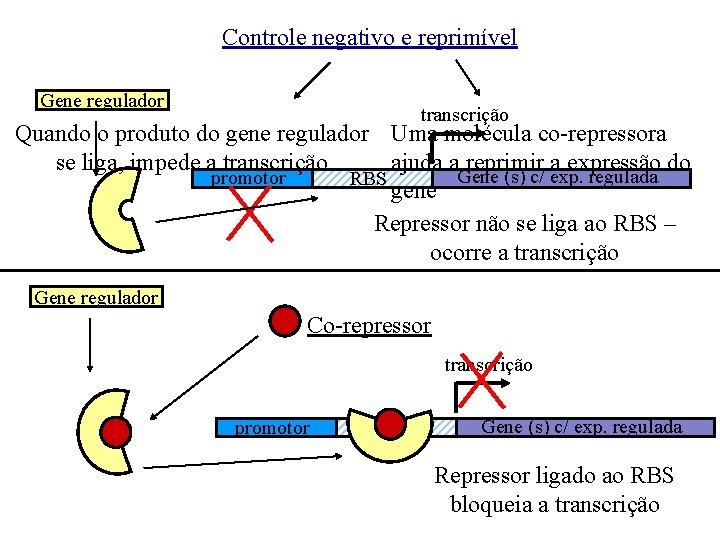
Controle negativo e reprimível Gene regulador transcrição Quando o produto do gene regulador Uma molécula co-repressora se liga, impede a transcrição ajuda a reprimir a expressão do Gene (s) c/ exp. regulada promotor RBS gene Repressor não se liga ao RBS – ocorre a transcrição Gene regulador Co-repressor transcrição promotor RBS Gene (s) c/ exp. regulada Repressor ligado ao RBS bloqueia a transcrição

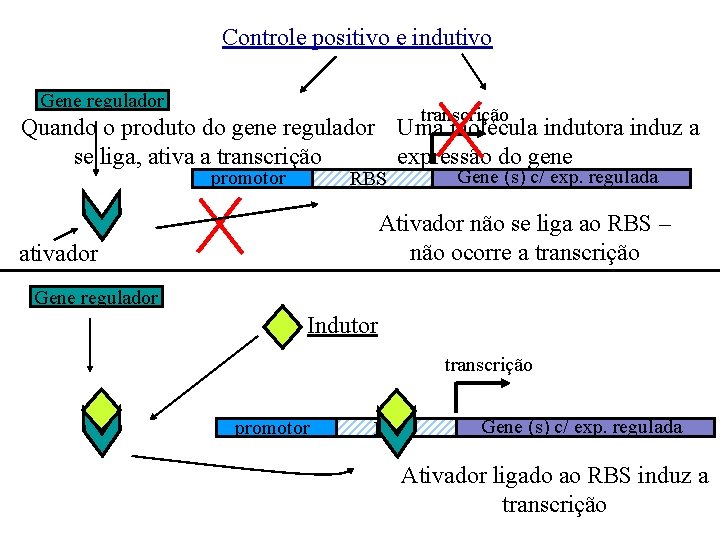
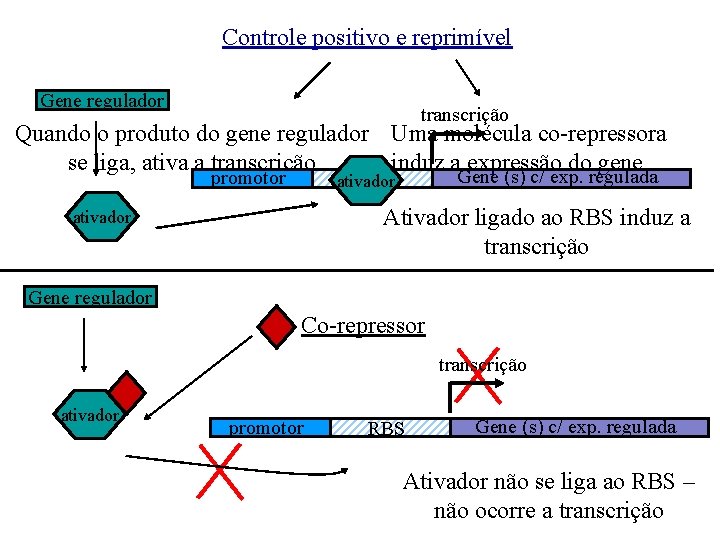
Controle positivo e indutivo Gene regulador transcrição Quando o produto do gene regulador Uma molécula indutora induz a se liga, ativa a transcrição expressão do gene promotor Gene (s) c/ exp. regulada RBS Ativador não se liga ao RBS – não ocorre a transcrição ativador Gene regulador Indutor transcrição promotor RBS Gene (s) c/ exp. regulada Ativador ligado ao RBS induz a transcrição

Controle positivo e reprimível Gene regulador transcrição Quando o produto do gene regulador Uma molécula co-repressora se liga, ativa a transcrição induz a expressão do gene promotor Gene (s) c/ exp. regulada RBS ativador Ativador ligado ao RBS induz a transcrição ativador Gene regulador Co-repressor transcrição ativador promotor RBS Gene (s) c/ exp. regulada Ativador não se liga ao RBS – não ocorre a transcrição

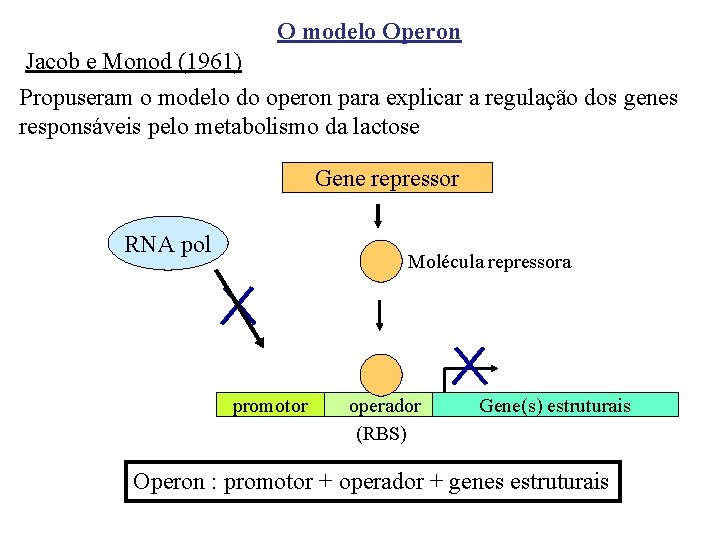
O modelo Operon Jacob e Monod (1961) Propuseram o modelo do operon para explicar a regulação dos genes responsáveis pelo metabolismo da lactose Gene repressor RNA pol Molécula repressora promotor operador (RBS) Gene(s) estruturais Operon : promotor + operador + genes estruturais

O operon lactose (lac) Principal fonte de energia da bactéria : glicose Na ausência de glicose, a bactéria pode usar a lactose As enzimas responsáveis pelo metabolismo da lactose só são produzidas em grande quantidade neste caso (uma qtde basal sempre é feita)

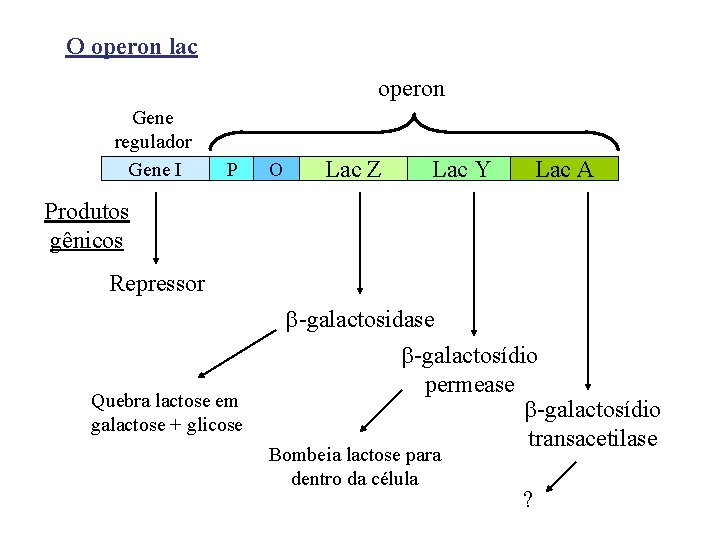
O operon lac operon Gene regulador Gene I P O Lac Z Lac Y Lac A Produtos gênicos Repressor Quebra lactose em galactose + glicose -galactosidase -galactosídio permease -galactosídio transacetilase Bombeia lactose para dentro da célula ?

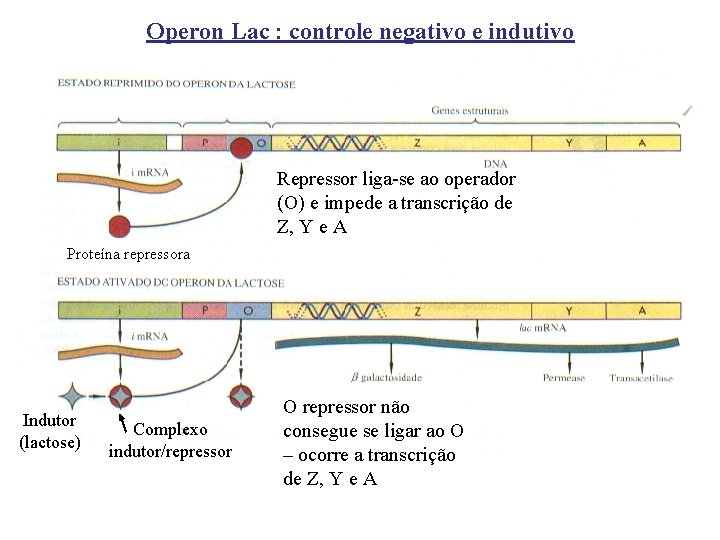
Operon Lac : controle negativo e indutivo Repressor liga-se ao operador (O) e impede a transcrição de Z, Y e A Proteína repressora Indutor (lactose) Complexo indutor/repressor O repressor não consegue se ligar ao O – ocorre a transcrição de Z, Y e A

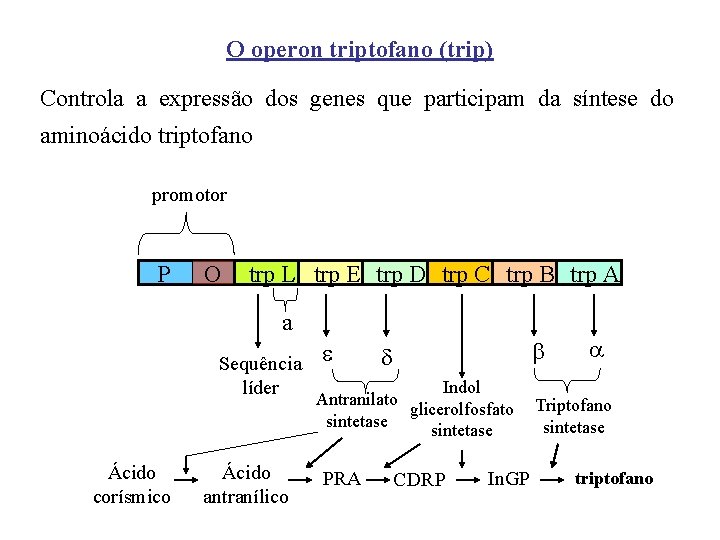
O operon triptofano (trip) Controla a expressão dos genes que participam da síntese do aminoácido triptofano promotor P O trp L trp E trp D trp C trp B trp A a Sequência líder Ácido corísmico Ácido antranílico Indol Antranilato glicerolfosfato sintetase PRA CDRP In. GP Triptofano sintetase triptofano

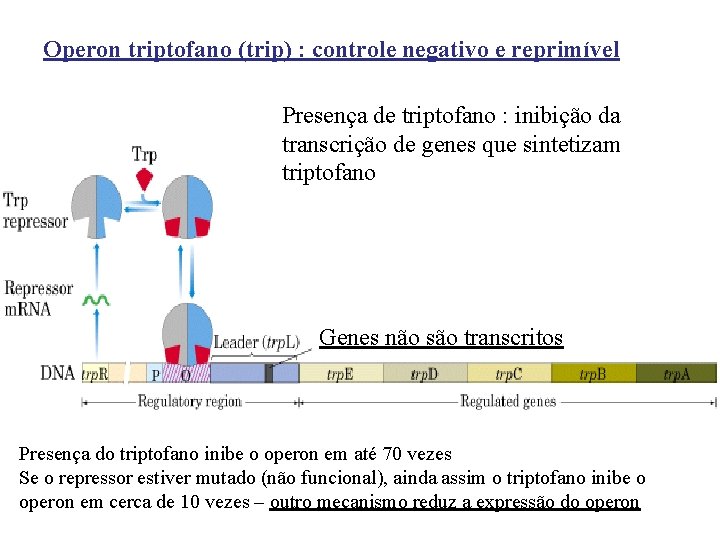
Operon triptofano (trip) : controle negativo e reprimível Presença de triptofano : inibição da transcrição de genes que sintetizam triptofano Genes não são transcritos Presença do triptofano inibe o operon em até 70 vezes Se o repressor estiver mutado (não funcional), ainda assim o triptofano inibe o operon em cerca de 10 vezes – outro mecanismo reduz a expressão do operon

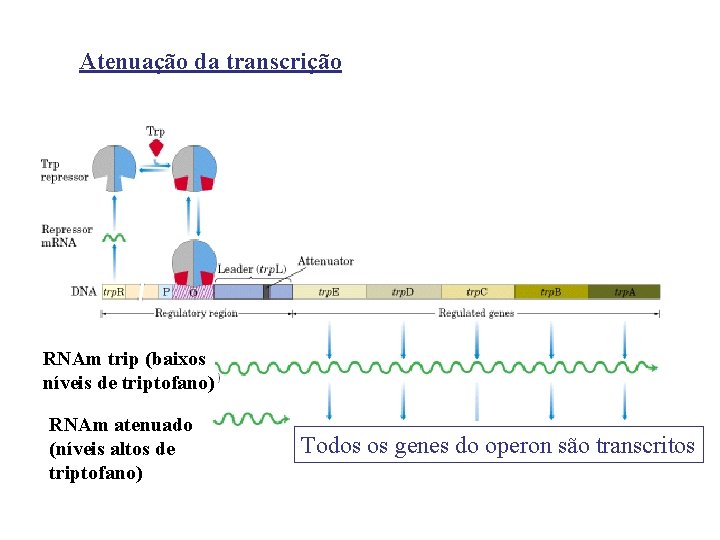
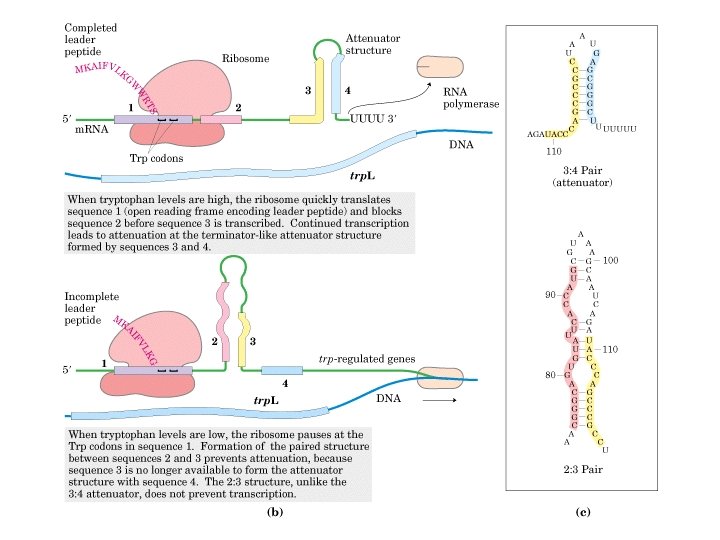
Atenuação da transcrição RNAm trip (baixos níveis de triptofano) RNAm atenuado (níveis altos de triptofano) Todos os genes do operon são transcritos

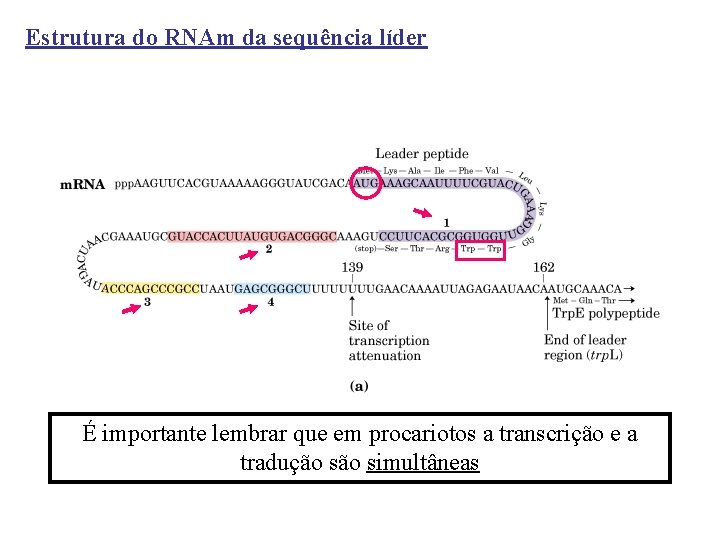
Estrutura do RNAm da sequência líder É importante lembrar que em procariotos a transcrição e a tradução simultâneas

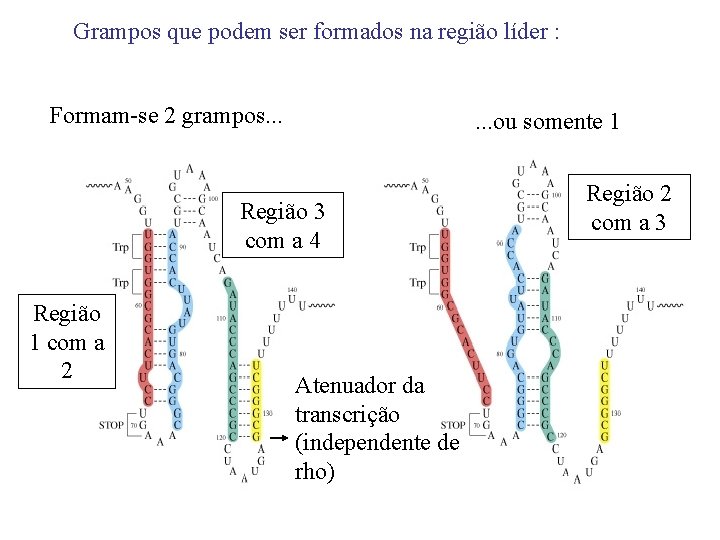
Grampos que podem ser formados na região líder : Formam-se 2 grampos. . . ou somente 1 Região 3 com a 4 Região 1 com a 2 Atenuador da transcrição (independente de rho) Região 2 com a 3


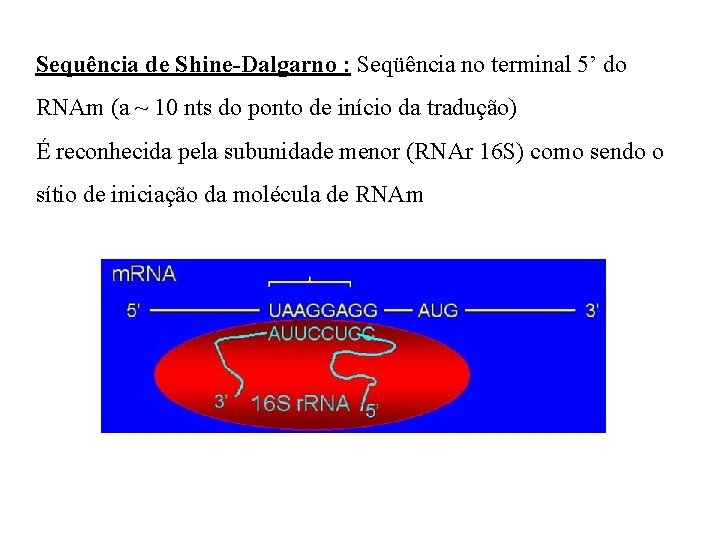
Sequência de Shine-Dalgarno : Seqüência no terminal 5’ do RNAm (a ~ 10 nts do ponto de início da tradução) É reconhecida pela subunidade menor (RNAr 16 S) como sendo o sítio de iniciação da molécula de RNAm

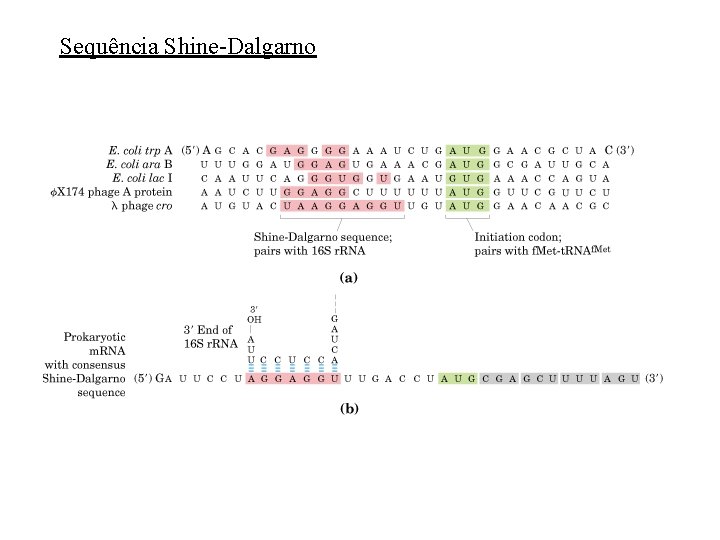
Sequência Shine-Dalgarno

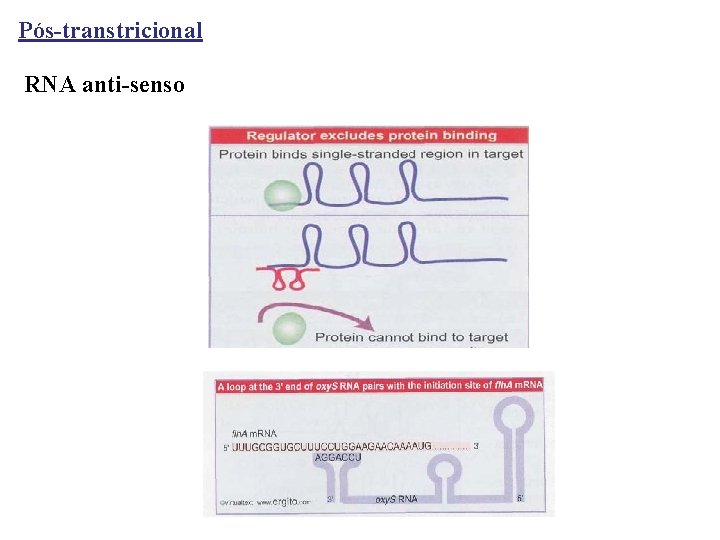
Pós-transtricional RNA anti-senso

Centro de Ciências Exatas e Natureza Departamento de Biologia Molecular Disciplina: Genética Molecular Bases Moleculares da Regulação Gênica Aula: Regulação da expressão gênica em Procarioto Eleonidas Moura Lima