Centro de Cincias Exatas e da Natureza Departamento











- Slides: 33

Centro de Ciências Exatas e da Natureza Departamento de Biologia Molecular Curso: Ciências Biológicas Disciplina: Genética Molecular Replicação do DNA Eleonidas Moura Lima

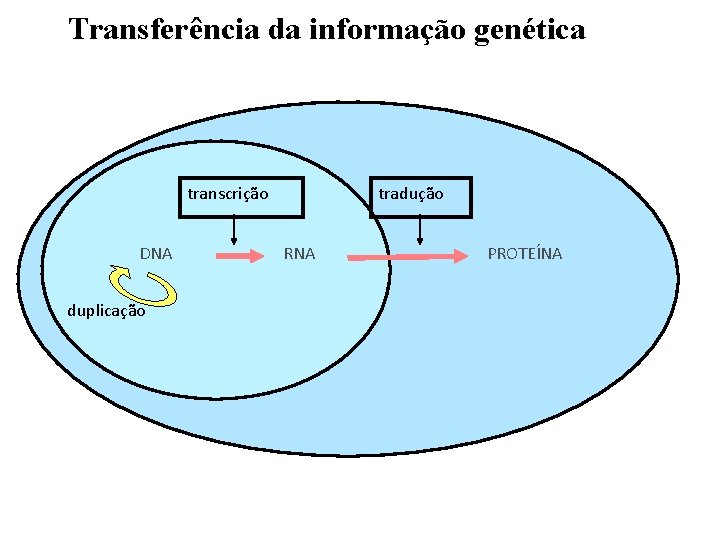
Transferência da informação genética transcrição DNA duplicação tradução RNA PROTEÍNA

REPLICAÇÃO DO DNA

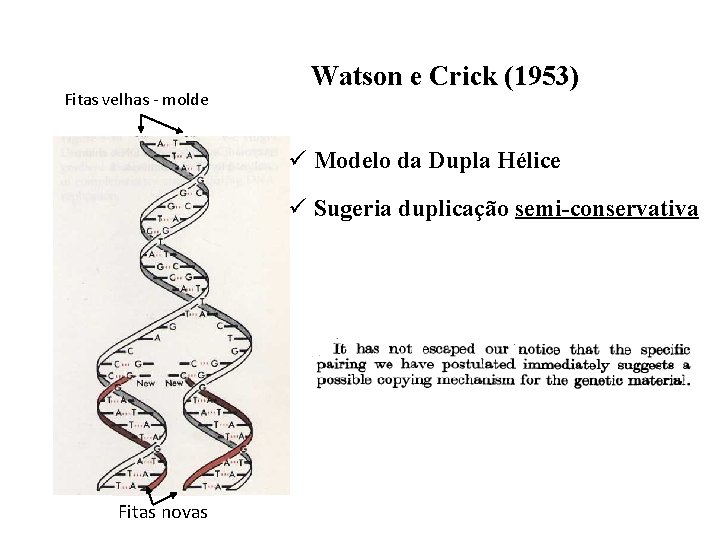
Fitas velhas - molde Watson e Crick (1953) ü Modelo da Dupla Hélice ü Sugeria duplicação semi-conservativa Fitas novas

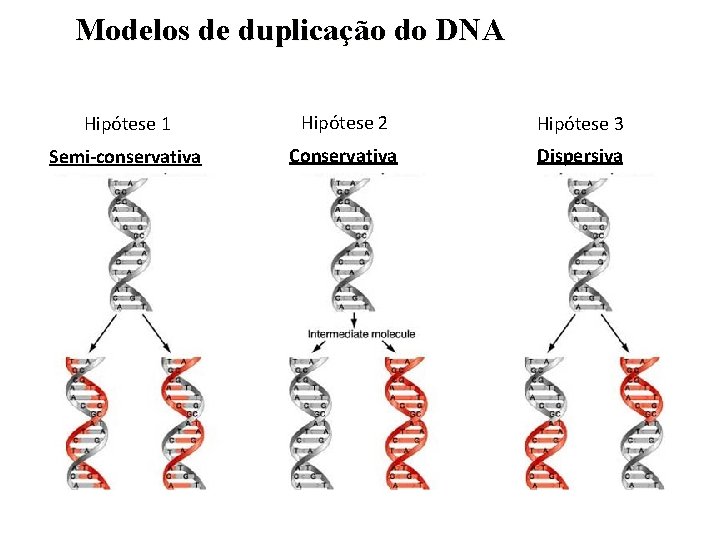
Modelos de duplicação do DNA Hipótese 1 Hipótese 2 Hipótese 3 Semi-conservativa Conservativa Dispersiva

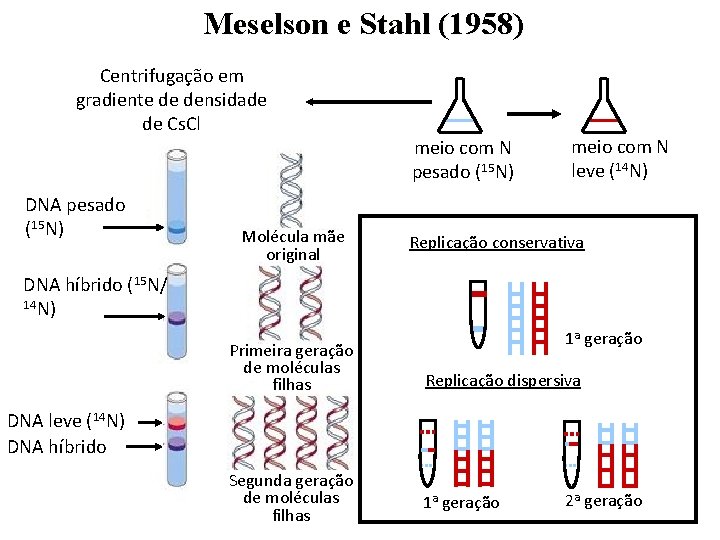
Meselson e Stahl (1958) Centrifugação em gradiente de densidade de Cs. Cl DNA pesado (15 N) Molécula mãe original meio com N pesado (15 N) meio com N leve (14 N) Replicação conservativa DNA híbrido (15 N/ 14 N) Primeira geração de moléculas filhas 1 a geração Replicação dispersiva DNA leve (14 N) DNA híbrido Segunda geração de moléculas filhas 1 a geração 2 a geração

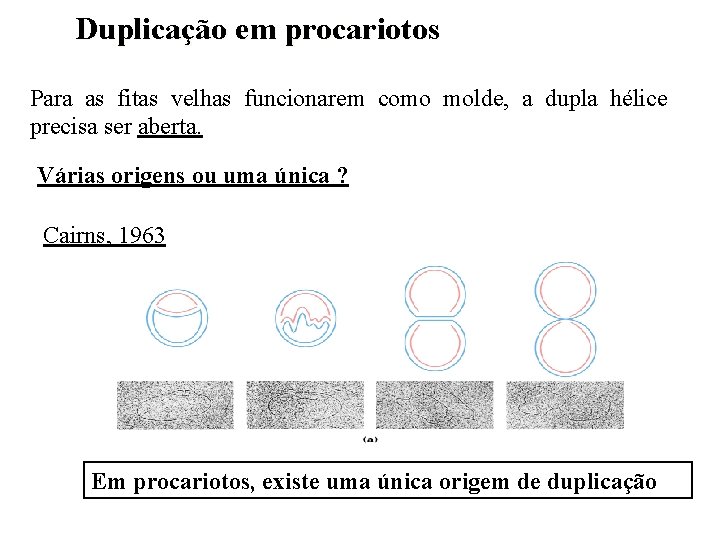
Duplicação em procariotos Para as fitas velhas funcionarem como molde, a dupla hélice precisa ser aberta. Várias origens ou uma única ? Cairns, 1963 Em procariotos, existe uma única origem de duplicação

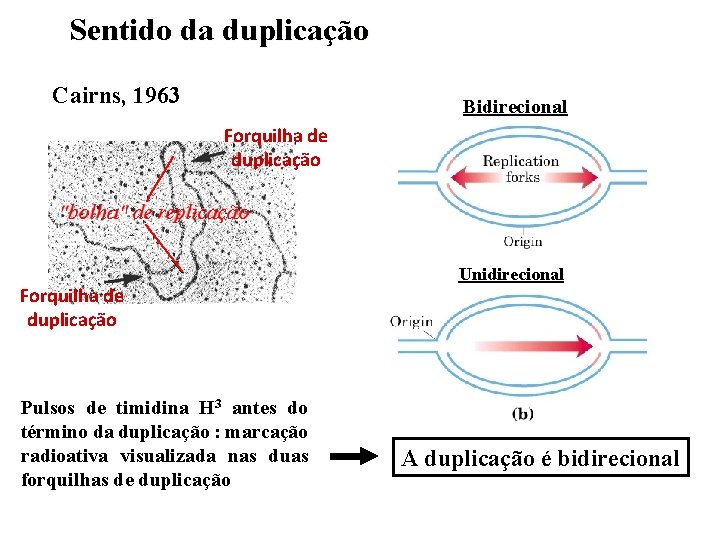
Sentido da duplicação Cairns, 1963 Bidirecional Forquilha de duplicação Pulsos de timidina H 3 antes do término da duplicação : marcação radioativa visualizada nas duas forquilhas de duplicação Unidirecional A duplicação é bidirecional

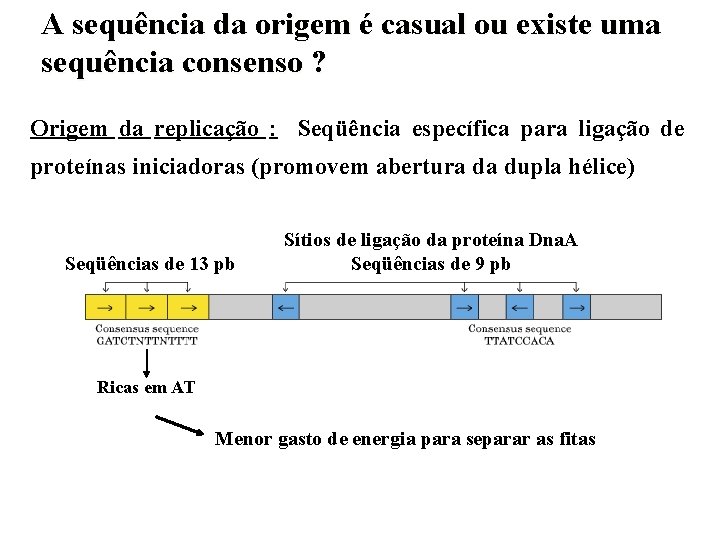
A sequência da origem é casual ou existe uma sequência consenso ? Origem da replicação : Seqüência específica para ligação de proteínas iniciadoras (promovem abertura da dupla hélice) Seqüências de 13 pb Sítios de ligação da proteína Dna. A Seqüências de 9 pb Ricas em AT Menor gasto de energia para separar as fitas

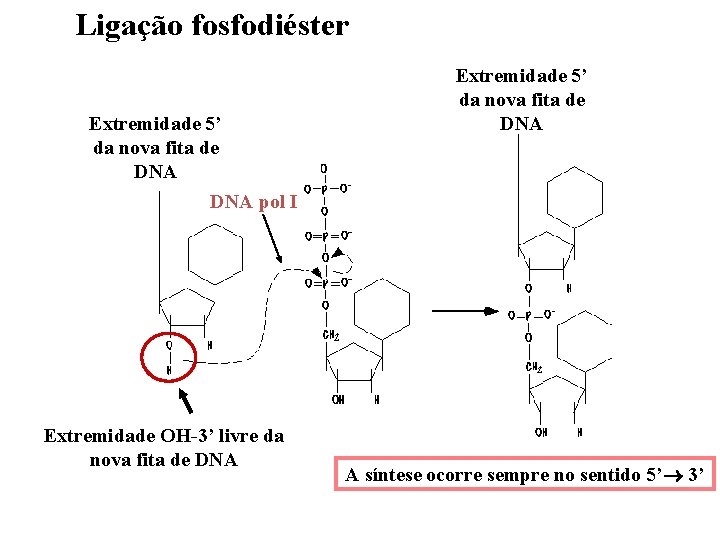
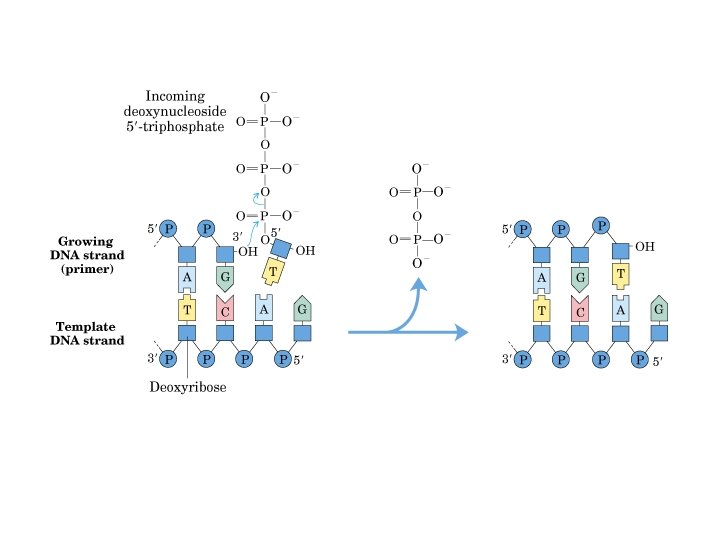
Uma vez que a dupla hélice está aberta, como é feita a síntese da nova fita ? DNA polimerases Kornberg (1957) : DNA polimerase I Requerimentos da DNA pol I para sintetizar nova fita de DNA : ü Desoxinucleotídeos trifosfatados ü Íons Mg 2+ ü DNA pré-existente, para servir como molde ü Uma extremidade OH-3’ de uma cadeia de DNA pré-existente para realizar a ligação fosfodiéster 10

Ligação fosfodiéster Extremidade 5’ da nova fita de DNA pol I Extremidade OH-3’ livre da nova fita de DNA Extremidade 5’ da nova fita de DNA A síntese ocorre sempre no sentido 5’ 3’

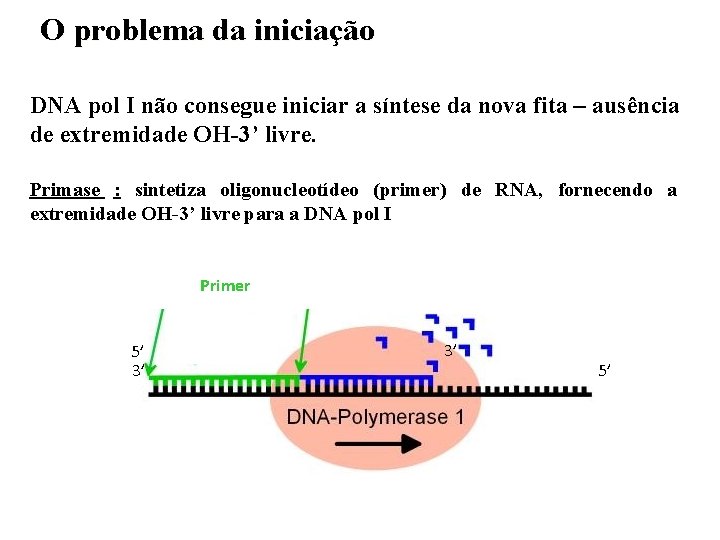
O problema da iniciação DNA pol I não consegue iniciar a síntese da nova fita – ausência de extremidade OH-3’ livre. Primase : sintetiza oligonucleotídeo (primer) de RNA, fornecendo a extremidade OH-3’ livre para a DNA pol I Primer 5’ 3’ 3’ 5’


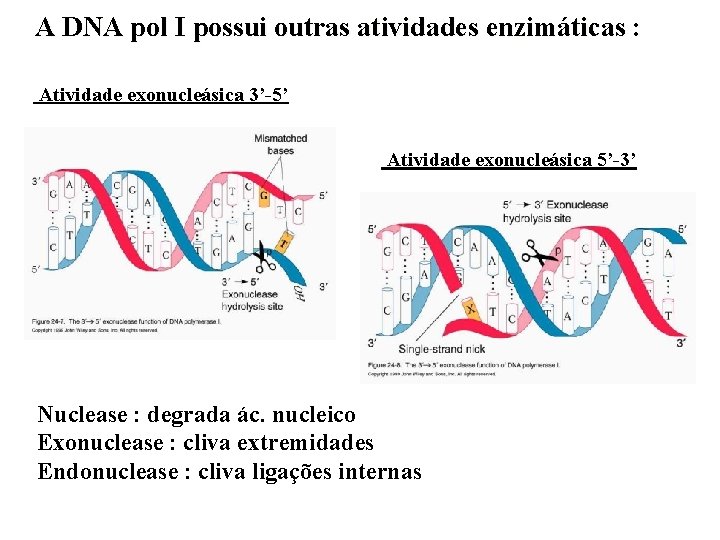
A DNA pol I possui outras atividades enzimáticas : Atividade exonucleásica 3’-5’ Atividade exonucleásica 5’-3’ Nuclease : degrada ác. nucleico Exonuclease : cliva extremidades Endonuclease : cliva ligações internas

Outras DNA polimerases foram descobertas : DNA pol II : • Reparo do DNA • Atividade polimerase 5’-3’ • Atividade exonuclease 3’ – 5’ DNA pol III : • Possui várias subunidades • Atividade polimerase 5’- 3’ • Atividade exonuclease 3’ – 5’ DNA polimerase IV e V – envolvidas em diferentes processos de reparo. 15

Processividade : habilidade da enzima de repetir a sua função catalítica sem dissociar-se do seu substrato Para a DNA pol : Definida pelo no médio de nt incorporados sem que a DNA pol se dissocie do DNA molde As DNA pol diferem em processividade

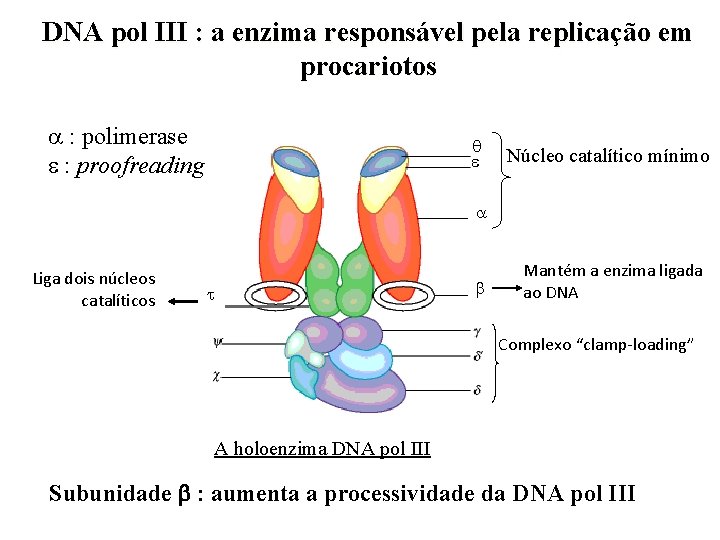
DNA pol III : a enzima responsável pela replicação em procariotos : polimerase : proofreading Núcleo catalítico mínimo Liga dois núcleos catalíticos Mantém a enzima ligada ao DNA Complexo “clamp-loading” A holoenzima DNA pol III Subunidade : aumenta a processividade da DNA pol III

Duplicação do DNA : um processo de alta fidelidade E. coli – 1 erro a ~ cada 109 bases adicionadas ou a após mil ou 10 mil eventos de replicação ü DNA polimerase tem um sítio ativo que só se fixa quando as bases estão pareadas corretamente ü DNA polimerase tem capacidade de verificar a fidelidade da replicação na cadeia nascente (proofreading) e corrigir os erros (atividades exonucleásicas) ü Depois da replicação, existe um sistema de reparo que corrige qualquer erro de pareamento de bases

Duplicação do DNA : um processo de alta fidelidade Pareamento incorreto : • Geometria diferente • Não acomoda-se no sítio ativo da DNA pol

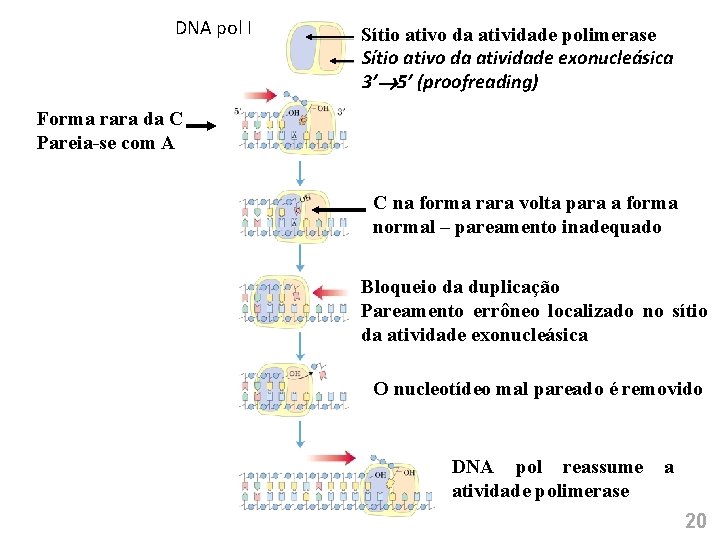
DNA pol I Sítio ativo da atividade polimerase Sítio ativo da atividade exonucleásica 3’ 5’ (proofreading) Forma rara da C Pareia-se com A C na forma rara volta para a forma normal – pareamento inadequado Bloqueio da duplicação Pareamento errôneo localizado no sítio da atividade exonucleásica O nucleotídeo mal pareado é removido DNA pol reassume atividade polimerase a 20

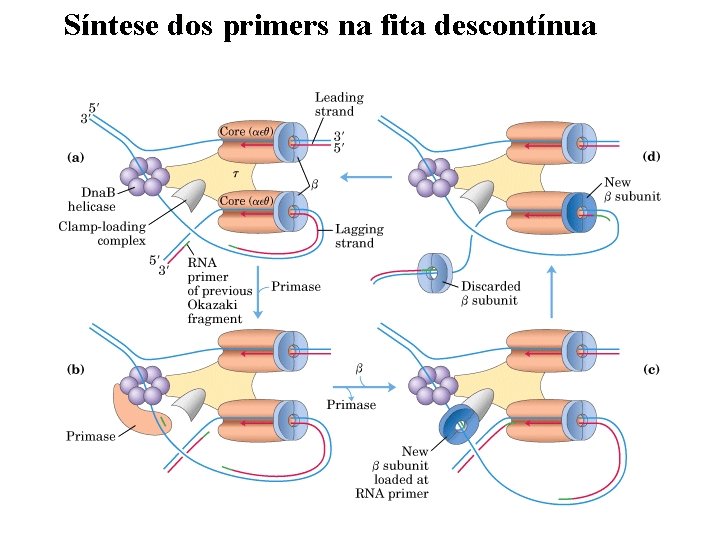
A síntese é contínua numa fita e descontínua na outra. . . 3’ 5’ 5’ 3’ 3’ 5’ Direção em que as fitas se estendem DNA pol só age no sentido 5’- 3’ !!! 3’ 5’ Direção em que as fitas se estendem 3’ 5’ Fita líder (contínua) 5’ 3’ 3’ 5’ Fita descontínua

Síntese dos primers na fita descontínua

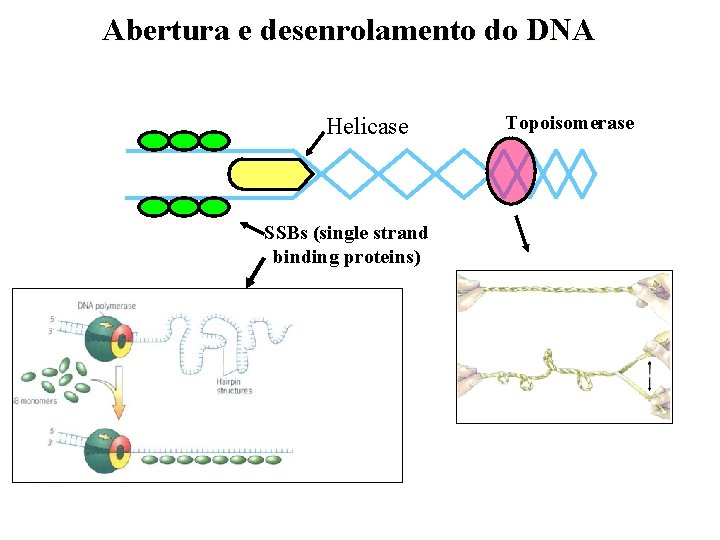
Abertura e desenrolamento do DNA Helicase SSBs (single strand binding proteins) Topoisomerase


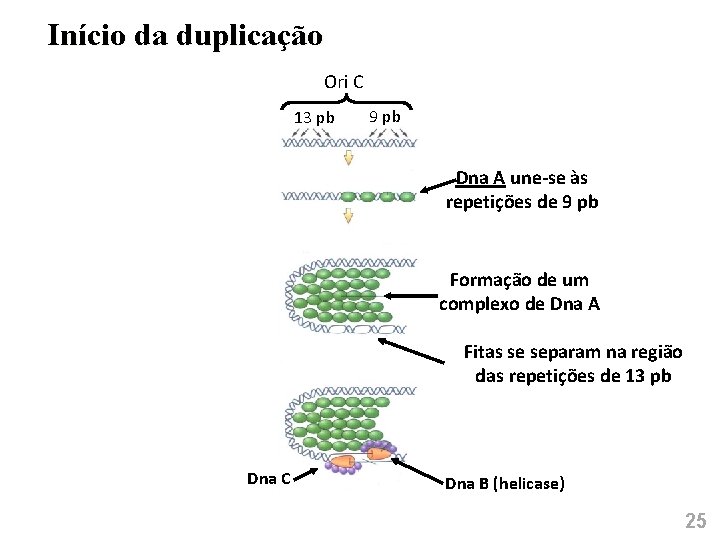
Início da duplicação Ori C 13 pb 9 pb Dna A une-se às repetições de 9 pb Formação de um complexo de Dna A Fitas se separam na região das repetições de 13 pb Dna C Dna B (helicase) 25

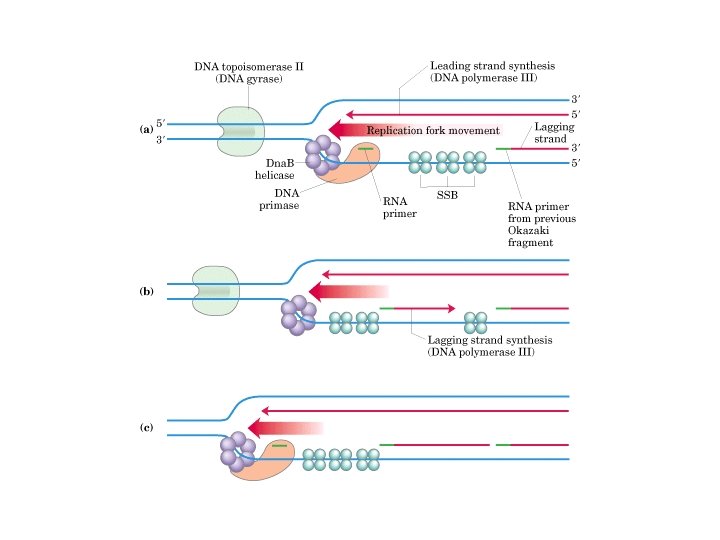
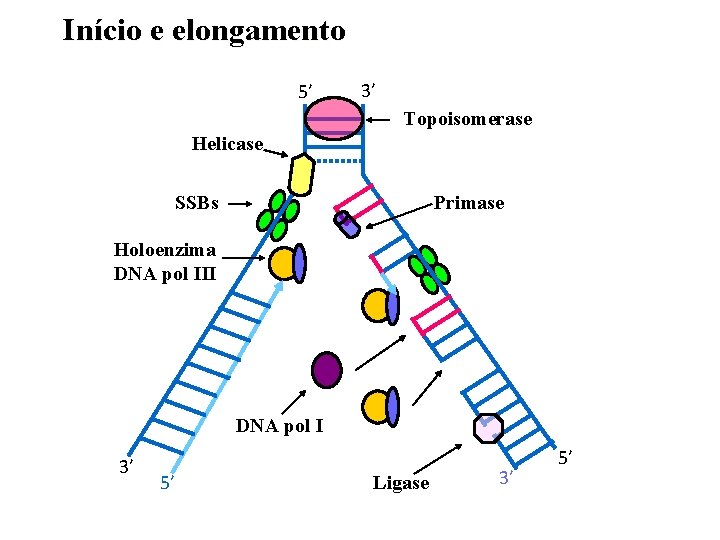
Início e elongamento 5’ 3’ Topoisomerase Helicase SSBs Primase Holoenzima DNA pol III DNA pol I 3’ 5’ Ligase 3’ 5’

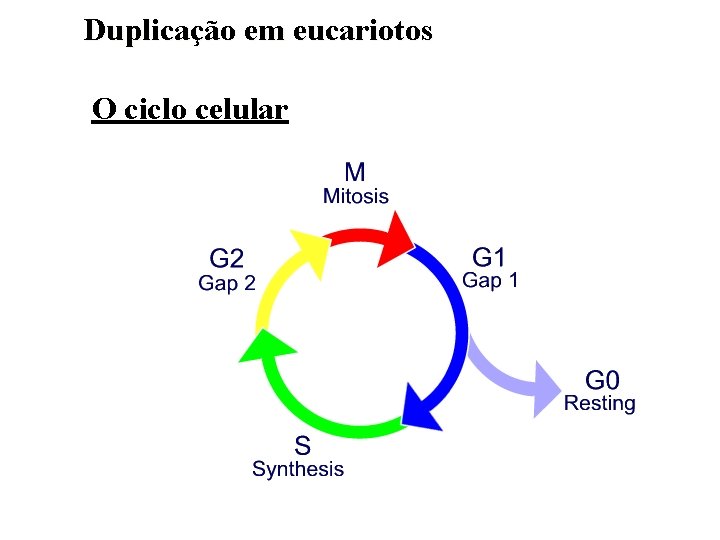
Duplicação em eucariotos O ciclo celular

Várias origens de duplicação Genoma humano – ~ 10 mil locais de origem (maior velocidade de replicação)

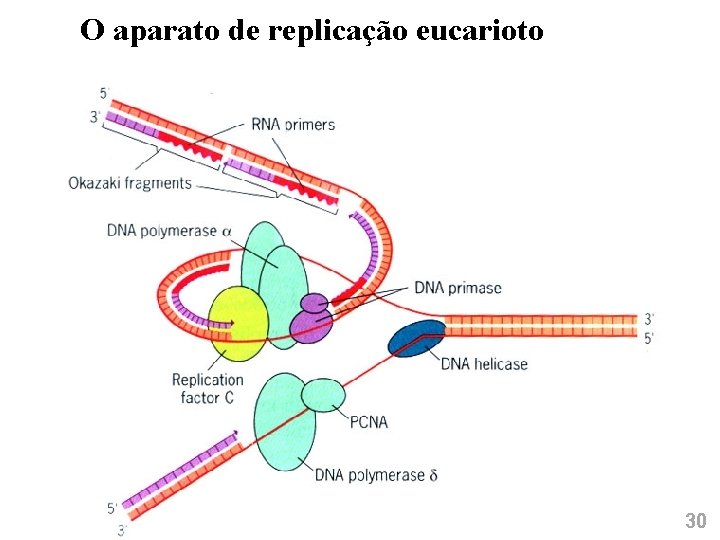
Tipos de DNA polimerases (Eucariotos) • POLIMERASE α - Núcleo - Atividade de polimerização e primase Fita descontínua - Sem atividade exonuclease 3’-5’ • POLIMERASE δ - Núcleo - Atividade de polimerização e exo 3’-5’ - Sem atividade primase • POLIMERASE ε - Núcleo - Atividade de exonuclease 3’-5’ (~ DNA Poli I) - Reparo de lesões provocadas por UV • RPA - Núcleo - Atividade semelhante à das SSB de procariotos • POLIMERASE γ - Mitocôndria - Replicação do genoma mitocondrial

O aparato de replicação eucarioto 30

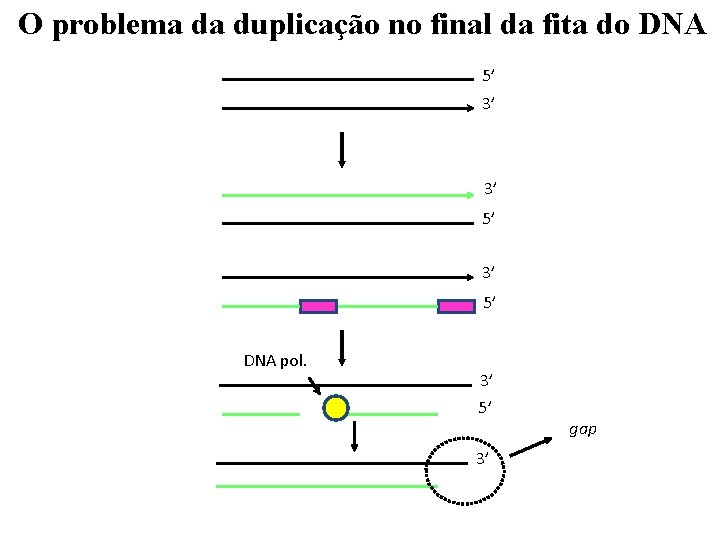
O problema da duplicação no final da fita do DNA 5’ 3’ 3’ 5’ DNA pol. 3’ 5’ 3’ gap

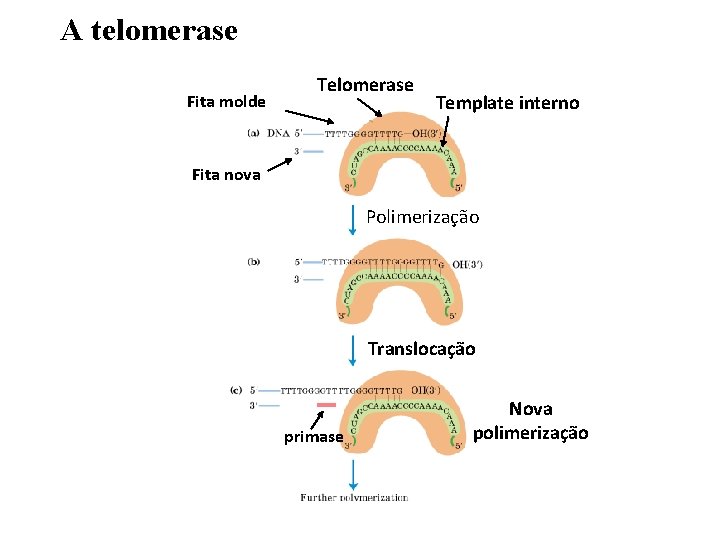
A telomerase Fita molde Telomerase Template interno Fita nova Polimerização Translocação primase Nova polimerização

Centro de Ciências Exatas e da Natureza Departamento de Biologia Molecular Curso: Ciências Biológicas Disciplina: Genética Molecular Replicação do DNA Bons Estudos Eleonidas Moura Lima