Caratteristiche di base della PCR 1 La PCR


Caratteristiche di base della PCR 1. La PCR e’ una metodica di clonaggio del DNA in sistemi non cellulari • la reazione standard di PCR e’ una amplificazione selettiva di DNA; • c’e specificita’ di amplificazione e di disegno dei primers - nested PCR - hot-start PCR - touch-down PCR

Scelta dei primers:

2. Maggiori vantaggi della PCR • velocita’ e facilita’ d’ uso • sensibilita’ • duttilita’

3. Maggiori svantaggi della PCR • si devono conoscere le sequenze fiancheggianti del DNA • ridotta dimensione e scarsa concentrazione dei prodotti di PCR • imprecisione nella replicazione del DNA 4. Spesso, per consentire ulteriori studi strutturali e funzionali, e’ necessario il clonaggio mediante cellule dei prodotti di PCR
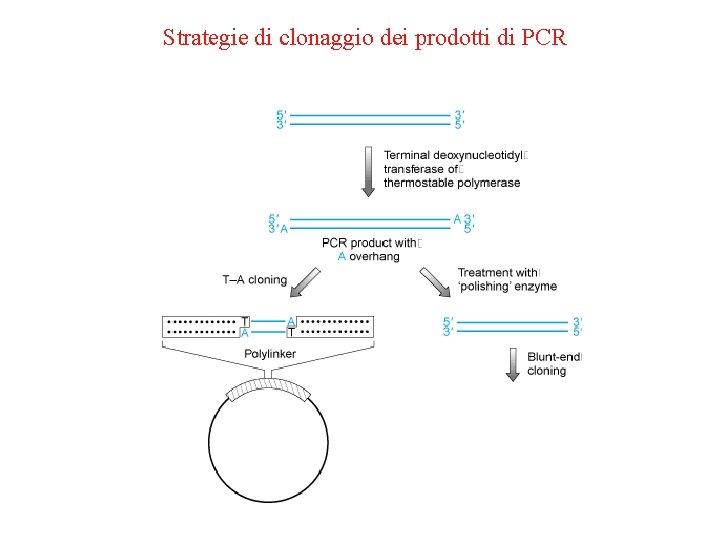
Strategie di clonaggio dei prodotti di PCR


Applicazioni della PCR: 1. La PCR permette la rapida amplificazione di uno specifico gene o esone di un gene come primo step per lo screening di mutazioni non caratterizzate. • amplificazioni per PCR di specifici esoni da DNA genomico • la RT-PCR puo’ essere usata per l’analisi dei trascritti

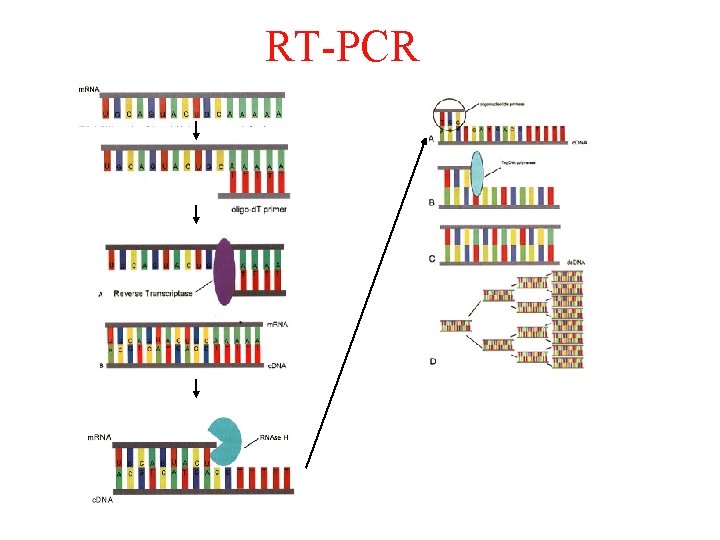
RT-PCR
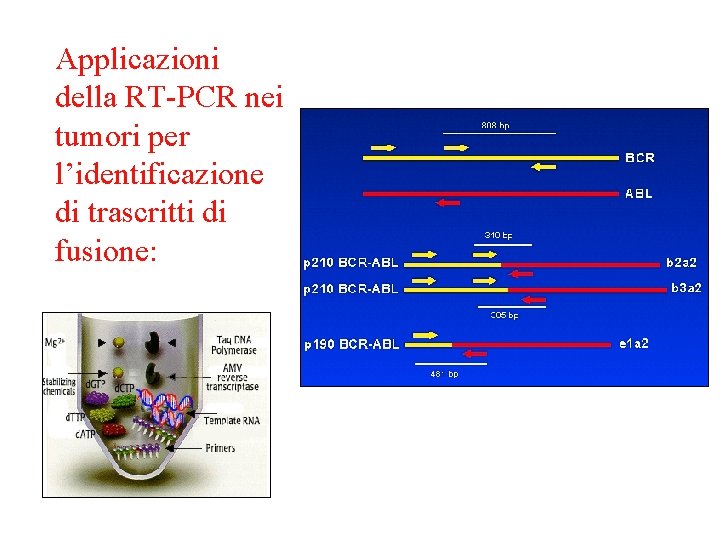
Applicazioni della RT-PCR nei tumori per l’identificazione di trascritti di fusione:
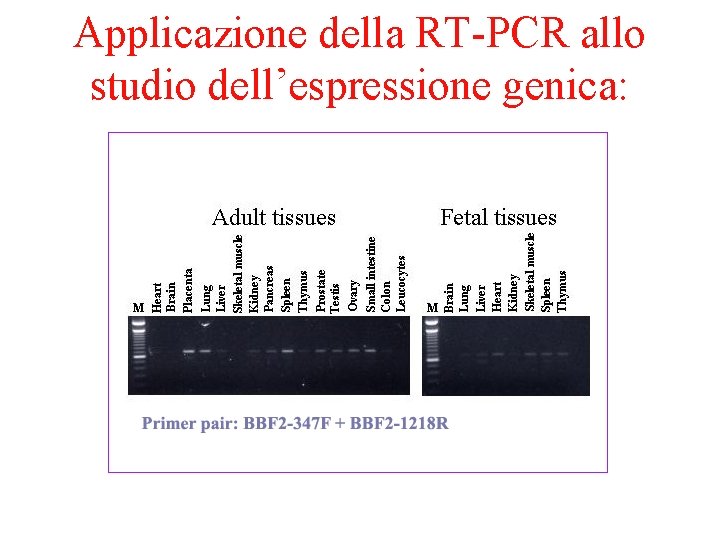
Applicazione della RT-PCR allo studio dell’espressione genica:
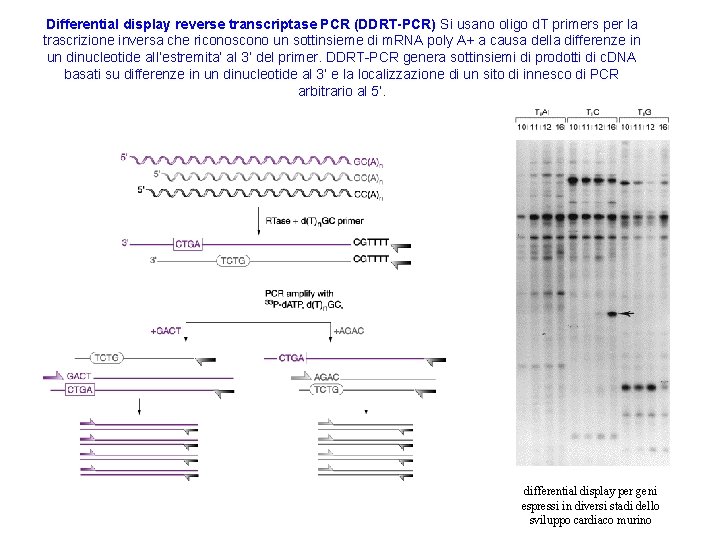
Differential display reverse transcriptase PCR (DDRT-PCR) Si usano oligo d. T primers per la trascrizione inversa che riconoscono un sottinsieme di m. RNA poly A+ a causa della differenze in un dinucleotide all’estremita’ al 3’ del primer. DDRT-PCR genera sottinsiemi di prodotti di c. DNA basati su differenze in un dinucleotide al 3’ e la localizzazione di un sito di innesco di PCR arbitrario al 5’. differential display per geni espressi in diversi stadi dello sviluppo cardiaco murino

2. La PCR permette la rapida genotipizzazione dei markers polimorfici • uso della PCR come alternativa per gli RFLP disegnando primers che fiancheggiano il sito di restrizione polimorfico. Successivamente all’amplificazione, il prodotto e’ digerito con l’enzima di restrizione. • uso della PCR per i polimorfismi Short tandem repeat (STRPs o microsatelliti ), disegnando primers da sequenze fiancheggianti i repeats.
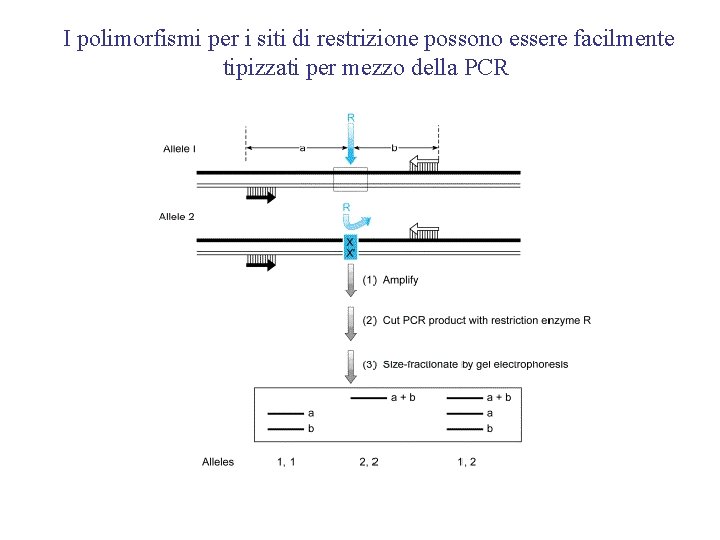
I polimorfismi per i siti di restrizione possono essere facilmente tipizzati per mezzo della PCR
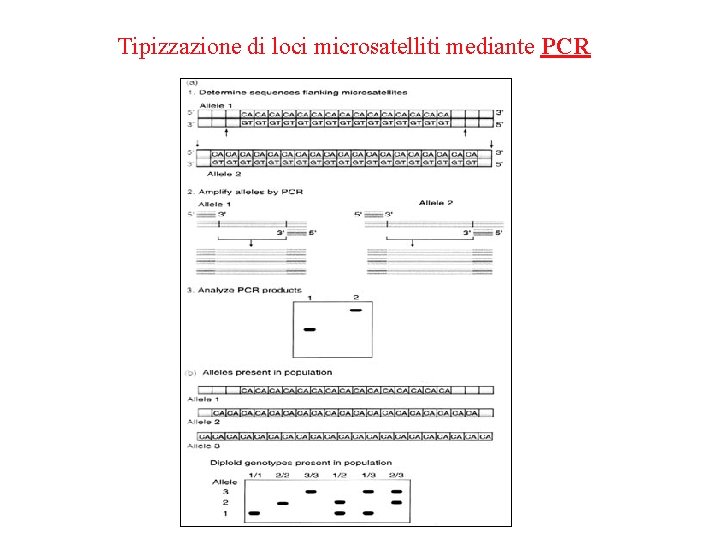
Tipizzazione di loci microsatelliti mediante PCR
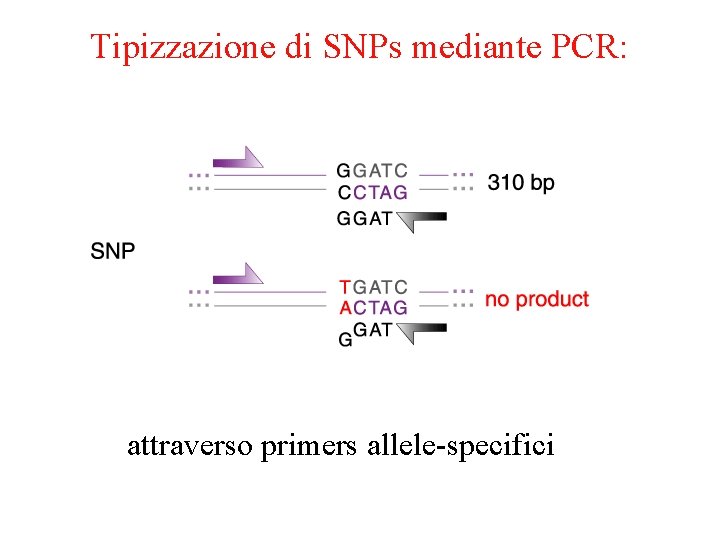
Tipizzazione di SNPs mediante PCR: attraverso primers allele-specifici

Applicazione della PCR per lo screening di ceppi patogeni e non patogeni di E. coli usando primers ceppo-specifici in PCR-Multiplex L’ uso della Real-Time RT-PCR quantitativa per rivelare genomi virali come HIV (AIDS), HCV (virus dell’epatite C) or HPV (human papilloma virus in associazione con il cancro all’utero) e’ un’altra applicazione diagnostica della PCR

3. La PCR puo’ essere usata per saggiare mutazioni note 4. a) discriminazione degli alleli per dimensione o suscettibilita’ 5. agli enzimi di restrizione: 6. - piccole delezioni o inserzioni in alleli possono 7. essere rivelate per PCR (come delezioni nell’allele 8. piu’ comune che causa la fibrosi cistica) 9. - una mutazione che cambia un sito di restrizione puo’ 10. essere rivelato mediante amplificazione seguita da 11. digestione enzimatica

Discriminazione degli alleli in base alla suscettibilita’ad un sito di restrizione introdotto artificialmente

• c) PCR allele-specifica (ARMS test) - possono essere disegnati due, uno specifico per l’allele mutante e l’altro specifico per l’allele wild-type. Il primer specifico per l’allele mutante termina al suo 3’ con la base mutante mentre il primer specifico per l’allele wild type termina con la sua base wild type al 3’. Questo methodo e’ usato per rivelare mutazioni specifiche e patogene, il cosiddetto amplification refractory mutation system (ARMS).
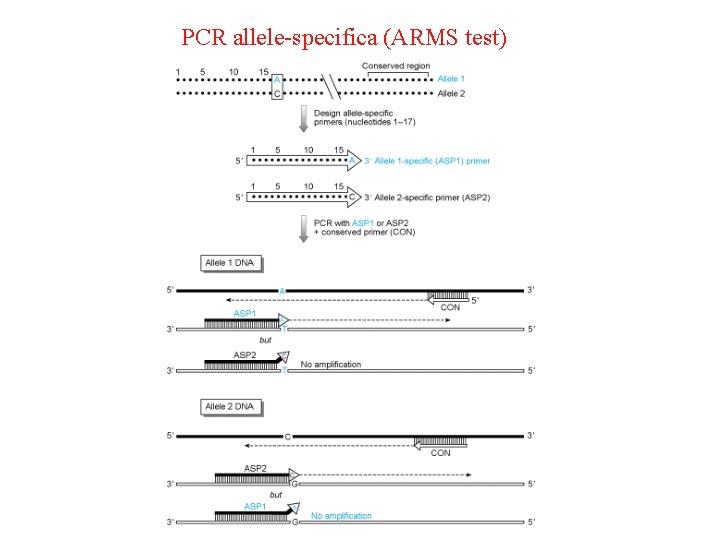
PCR allele-specifica (ARMS test)
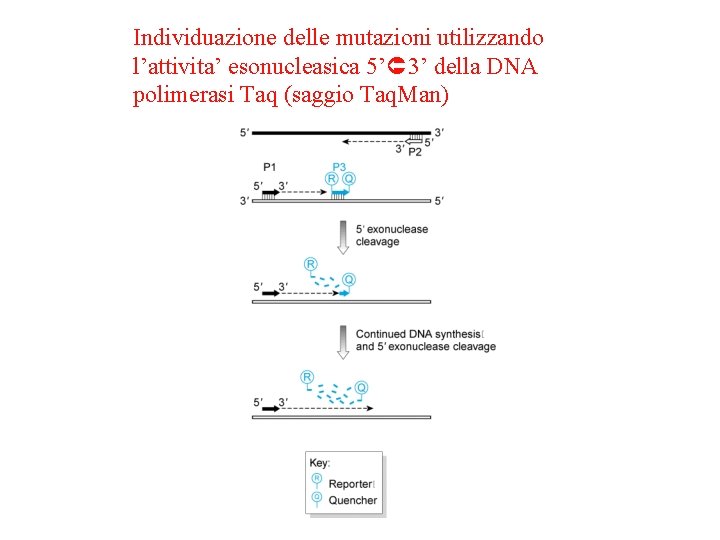
Individuazione delle mutazioni utilizzando l’attivita’ esonucleasica 5’ 3’ della DNA polimerasi Taq (saggio Taq. Man)

4. PCR indiscriminata - la DOP-PCR permette il clonaggio del DNA usando oligonucleotidi degenerati. - la Linker-primed PCR (ligation adaptor PCR) permette l’amplificazione indiscriminata ed il clonaggio di sequenze di DNA.
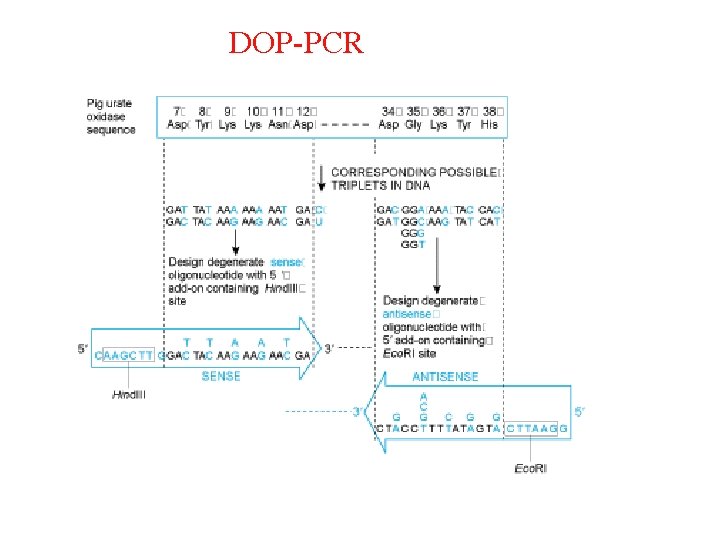
DOP-PCR

Linker-primed PCR

5. La PCR con sequenze ancorate (Anchored PCR) e’ usata per fare ‘genomic walking’ partendo da una sequenza nota nel genoma - questo e’ un metodo utile per clonare sequenze regolative al 5’ di un gene (promotore) di un gene di cui e’ nota la sequenza completa del c. DNA.
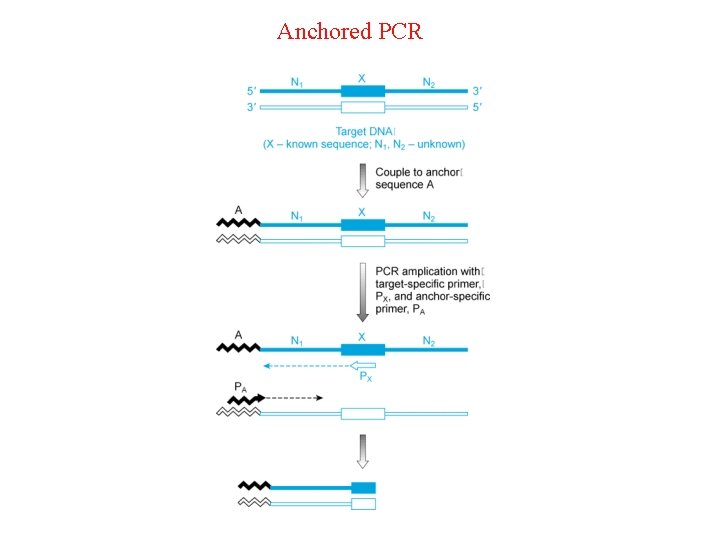
Anchored PCR
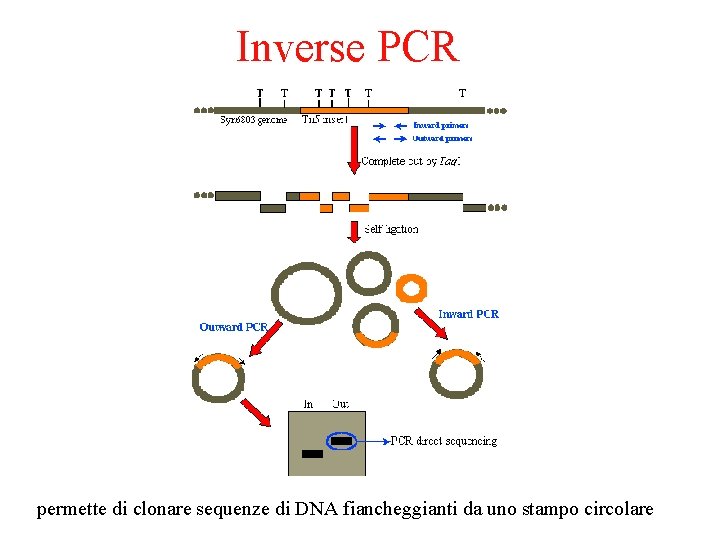
Inverse PCR permette di clonare sequenze di DNA fiancheggianti da uno stampo circolare


6. Clonaggio di c. DNA a lunghezza completa: • RACE (rapid amplification of c. DNA ends) che permette di amplificare la sequenza compresa tra una regione precedentemente caratterizzata nell’m. RNA (c. DNA) e una sequenza “àncora” accoppiata all’estremità 3’ o 5’.
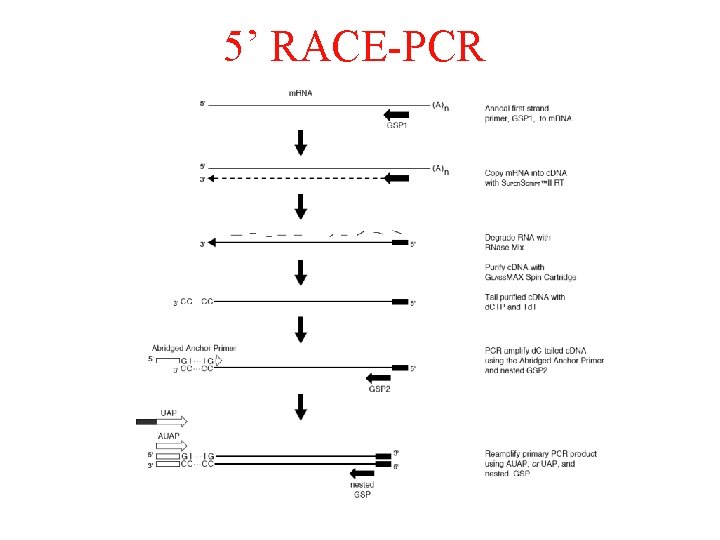
5’ RACE-PCR
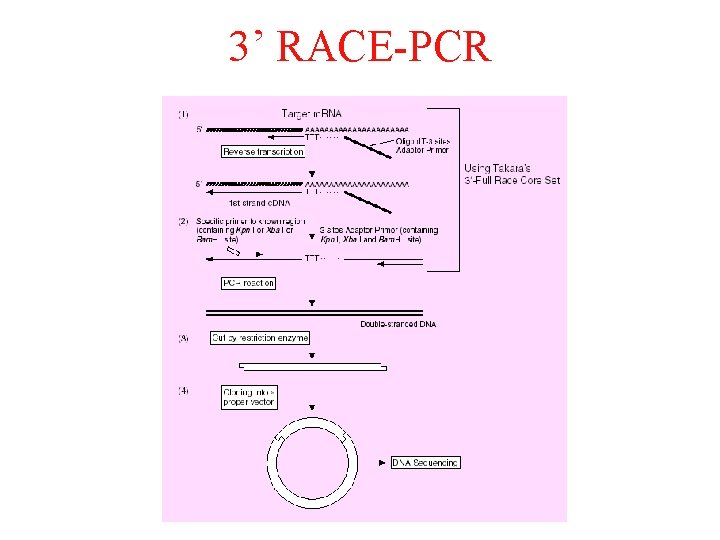
3’ RACE-PCR

7. Sequenziamento ciclico
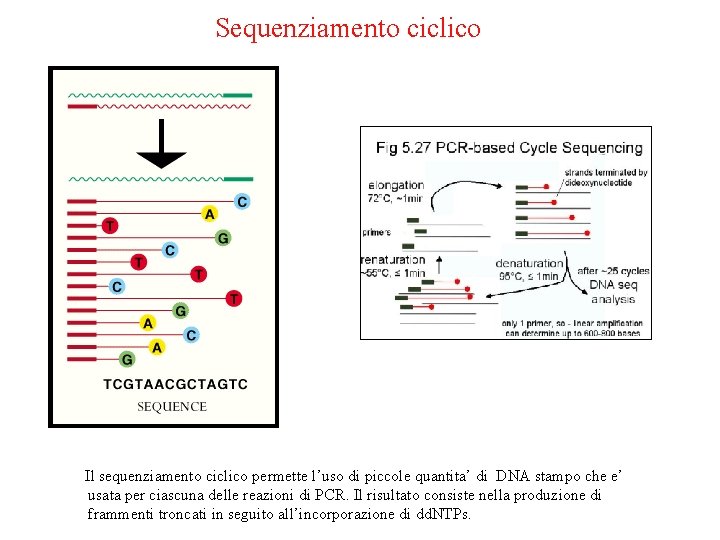
Sequenziamento ciclico Il sequenziamento ciclico permette l’uso di piccole quantita’ di DNA stampo che e’ usata per ciascuna delle reazioni di PCR. Il risultato consiste nella produzione di frammenti troncati in seguito all’incorporazione di dd. NTPs.
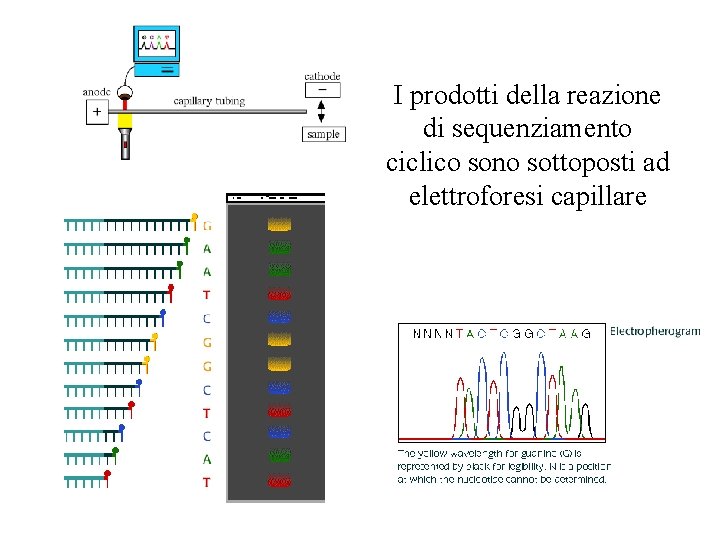
I prodotti della reazione di sequenziamento ciclico sono sottoposti ad elettroforesi capillare

8. Mutagenesi sito-diretta in vitro

Mutagenesi mediante PCR con aggiunta di una sequenza in 5’ Le estremita’ dei prodotti di PCR si possono facilmente manipolare. Ad esempio, si possono aggiungere siti di restrizione per rendere piu’ semplice il clonaggio dei prodotti

. . . altra strategia. . mutazioni specifiche possono essere anche introdotte al centro di una molecola di DNA durante la PCR
- Slides: 39