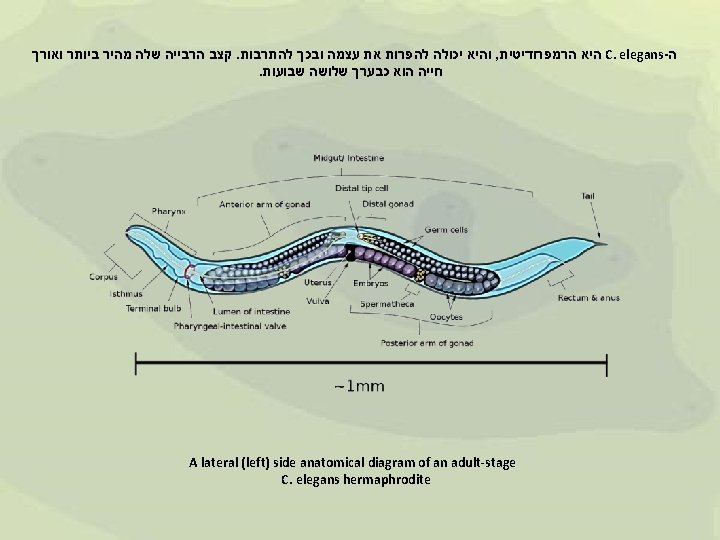
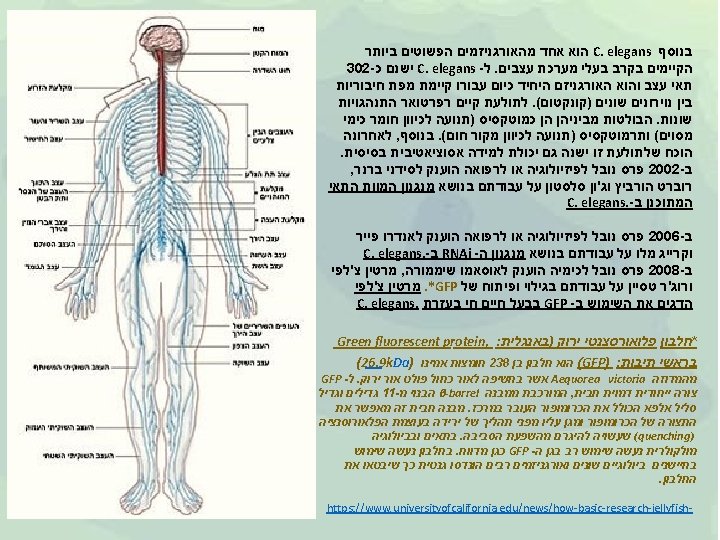
C elegans Caenorhabditis elegans Wildtype C elegans hermaphrodite

C. elegans Caenorhabditis elegans Wild-type C. elegans hermaphrodite stained with the fluorescent dye Texas Red to highlight the nuclei of all cells PPS 1 - חלק ראשון


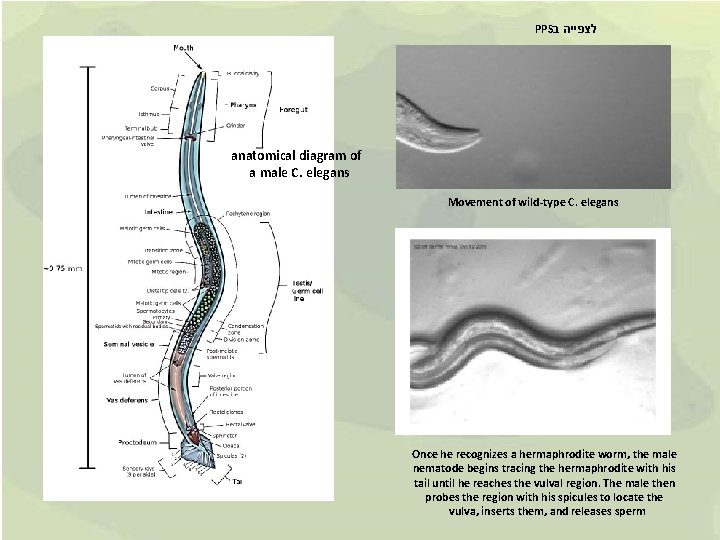
PPS לצפייה ב anatomical diagram of a male C. elegans Movement of wild-type C. elegans Once he recognizes a hermaphrodite worm, the male nematode begins tracing the hermaphrodite with his tail until he reaches the vulval region. The male then probes the region with his spicules to locate the vulva, inserts them, and releases sperm

C. elegans research has contributed a lot to science, so much so that it has helped win three Nobel prizes: 2002 & 2006 in physiology or medicine and 2008 in Chemistry https: //twitter. com/ellie_elegans

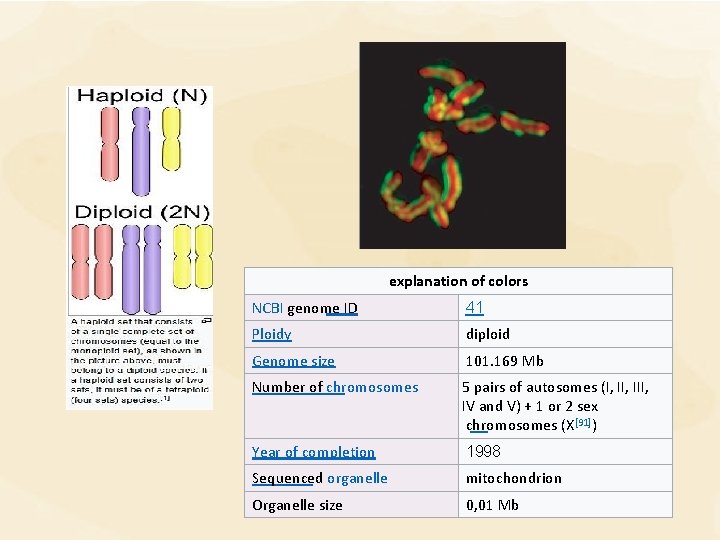
explanation of colors NCBI genome ID 41 Ploidy diploid Genome size 101. 169 Mb Number of chromosomes 5 pairs of autosomes (I, III, IV and V) + 1 or 2 sex chromosomes (X[91]) Year of completion 1998 Sequenced organelle mitochondrion Organelle size 0, 01 Mb
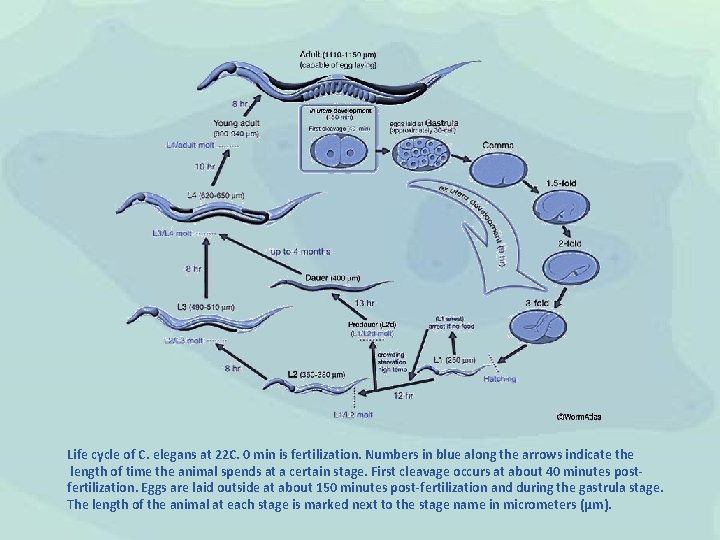
Life cycle of C. elegans at 22 C. 0 min is fertilization. Numbers in blue along the arrows indicate the length of time the animal spends at a certain stage. First cleavage occurs at about 40 minutes postfertilization. Eggs are laid outside at about 150 minutes post-fertilization and during the gastrula stage. The length of the animal at each stage is marked next to the stage name in micrometers (μm).
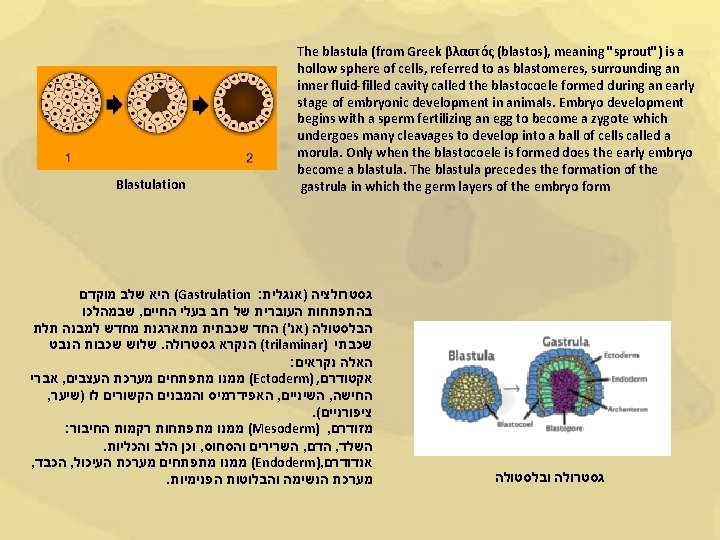
Blastulation The blastula (from Greek βλαστός (blastos), meaning "sprout") is a hollow sphere of cells, referred to as blastomeres, surrounding an inner fluid-filled cavity called the blastocoele formed during an early stage of embryonic development in animals. Embryo development begins with a sperm fertilizing an egg to become a zygote which undergoes many cleavages to develop into a ball of cells called a morula. Only when the blastocoele is formed does the early embryo become a blastula. The blastula precedes the formation of the gastrula in which the germ layers of the embryo form ( היא שלב מוקדם Gastrulation : גסטרולציה )אנגלית שבמהלכו , בהתפתחות העוברית של רוב בעלי החיים הבלסטולה )אנ'( החד שכבתית מתארגנת מחדש למבנה תלת שלוש שכבות הנבט. ( הנקרא גסטרולה trilaminar) שכבתי : האלה נקראים אברי , ( ממנו מתפתחים מערכת העצבים Ectoderm) , אקטודרם , האפידרמיס והמבנים הקשורים לו )שיער , השיניים , החישה . ( ציפורניים : ( ממנו מתפתחות רקמות החיבור Mesoderm) , מזודרם . וכן הלב והכליות , השרירים והסחוס , הדם , השלד , הכבד , ( ממנו מתפתחים מערכת העיכול Endoderm), אנדודרם . מערכת הנשימה והבלוטות הפנימיות גסטרולה ובלסטולה

This is a view of the physical map of the genome as displayed in the genome database ACe. DB. The longer lines at the top are YAC clones (their names start with a Y). The shorter items below are cosmid clones. The bold YACs are ones used in mapping c. DNAs to the genome. The yellow boxed cosmids are those sequenced. Cosmids with a following * are ones that are canonical for a set of smaller cosmids, that are not displayed. The yellow bar at the bottom represents the sequenced DNA. The triangles indicate points of transposon insertion in strains of C. elegans. The C. elegans physical map was constructed in two phases. Firstly approximately 17, 000 cosmid clones (insert size 35 kb) were fingerprinted, and contiguated using fingerprint ovelap data. Secondly, selected cosmid clones were mapped to a 3, 000 clone yeast artificial chromosome library (insert size >150 kb to 1 Mb) by hybridisation. This served to link and order the cosmid contigs, and has yielded a map which has only a handful of "gaps" (regions not covered by cloned DNAs).

Esta es una vista del mapa físico del genoma como se muestra en la base de datos del genoma ACe. DB. Las líneas más largas en la parte superior son clones YAC (sus nombres comienzan con una Y). Los artículos más cortos a continuación son clones de cósmidos. Los YAC en negrita son los que se usan para mapear los ADNc al genoma. Los cósmidos en caja amarilla son los secuenciados. Los cósmidos con un siguiente * son los que son canónicos para un conjunto de cósmidos más pequeños, que no se muestran. La barra amarilla en la parte inferior representa el ADN secuenciado. Los triángulos indican puntos de inserción de transposones en cepas de C. elegans. El mapa físico de C. elegans se construyó en dos fases. En primer lugar, se tomaron huellas digitales de aproximadamente 17, 000 clones de cósmidos (tamaño de inserción de 35 kb) y se contiguaron utilizando datos de superposición de huellas digitales. En segundo lugar, los clones de cósmidos seleccionados se mapearon en una biblioteca de cromosomas artificiales de levadura de 3. 000 clones (tamaño de inserción> 150 kb a 1 Mb) por hibridación. Esto sirvió para vincular y ordenar los contiguos cósmidos, y ha producido un mapa que tiene solo un puñado de "huecos" (regiones no cubiertas por ADN clonados).

The cosmid fingerprinting was achieved by restricting each with Hin. D III, labelling the fragment ends with 32 -P, and cutting with a second, frequent-cutting enzyme (Sau 3 A I). The labelled fragments were analysed by acrylamide gel electrophoresis, and the resulting autoradiographs digitised. These digital fingerprints were then examined using custom-written software to identify clones which shared significant overlap, and contigs of overlapping clones were built up. This process resulted in over 600 contigs*, some of only a very few clones. These contigs were mapped to the YAC library by selecting marker cosmids spanning each contig and hybridising them to high density YAC library filters. This process resulted in a massive reduction in the number of contigs, to the current position where over 99% of the genome is covered by either YAC and/or cosmid clones. The use of two different host-vector systems appears to have been very succesfull in getting round problems of "unclonable" DNA: segments of the genome which can be propagated only poorly (if at all) in one system appear to be stable in the other. *A contig (from contiguous) is a set of overlapping DNA segments that together represent a consensus region of DNA. [1] In bottomup sequencing projects, a contig refers to overlapping sequence data (reads); [2] in top-down sequencing projects, contig refers to the overlapping clones that form a physical map of the genome that is used to guide sequencing and assembly. La huella digital de cósmidos se logró restringiendo cada uno con Hin. D III, marcando los extremos del fragmento con 32 -P y cortando con una segunda enzima de corte frecuente (Sau 3 A I). Los fragmentos marcados se analizaron por electroforesis en gel de acrilamida y las autorradiografías resultantes se digitalizaron. Luego se examinaron estas huellas digitales usando un software escrito a medida para identificar clones que compartían una superposición significativa, y se construyeron segmentos de clones superpuestos. Este proceso dio como resultado más de 600 contigs*, algunos de solo unos pocos clones. Estos contigs se mapearon a la biblioteca YAC seleccionando cósmidos marcadores que abarcan cada contig e hibridándolos a filtros de biblioteca YAC de alta densidad. Este proceso resultó en una reducción masiva en el número de contigs, a la posición actual donde más del 99% del genoma está cubierto por clones YAC y / o cósmidos. El uso de dos sistemas diferentes de huésped-vector parece haber sido muy exitoso para solucionar problemas de ADN "no clonable": los segmentos del genoma que pueden propagarse solo pobremente (si es que lo hacen) en un sistema parecen ser estables en el otro. *Un Cóntigo, 1 en inglés Contig (de contiguous), son segmentos de ADN superpuestos, que juntos representan una región consenso de ADN. 2 En la secuenciación de "abajo arriba", un cóntigo refiere a la superposición de datos en la secuencia, en la secuenciación de "arriba abajo", refiere a los clones superpuestos que forman un mapa físico del genoma utilizado para guiar la secuenciación y ensamblaje de este
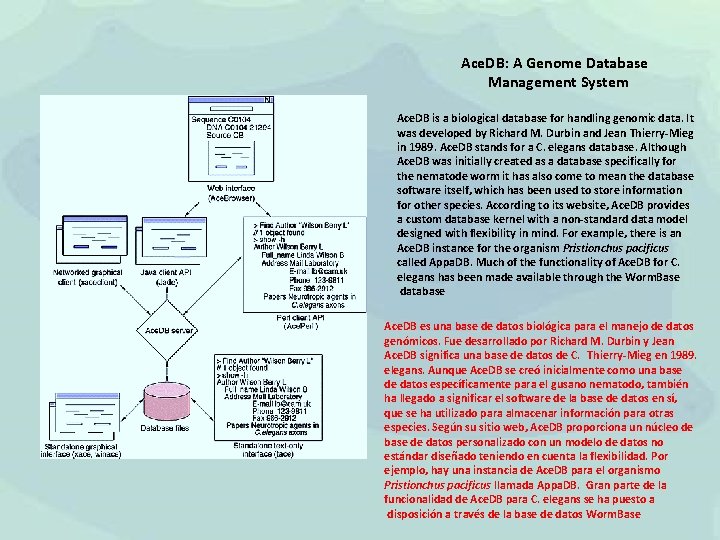
Ace. DB: A Genome Database Management System Ace. DB is a biological database for handling genomic data. It was developed by Richard M. Durbin and Jean Thierry-Mieg in 1989. Ace. DB stands for a C. elegans database. Although Ace. DB was initially created as a database specifically for the nematode worm it has also come to mean the database software itself, which has been used to store information for other species. According to its website, Ace. DB provides a custom database kernel with a non-standard data model designed with flexibility in mind. For example, there is an Ace. DB instance for the organism Pristionchus pacificus called Appa. DB. Much of the functionality of Ace. DB for C. elegans has been made available through the Worm. Base database Ace. DB es una base de datos biológica para el manejo de datos genómicos. Fue desarrollado por Richard M. Durbin y Jean Ace. DB significa una base de datos de C. Thierry-Mieg en 1989. elegans. Aunque Ace. DB se creó inicialmente como una base de datos específicamente para el gusano nematodo, también ha llegado a significar el software de la base de datos en sí, que se ha utilizado para almacenar información para otras especies. Según su sitio web, Ace. DB proporciona un núcleo de base de datos personalizado con un modelo de datos no estándar diseñado teniendo en cuenta la flexibilidad. Por ejemplo, hay una instancia de Ace. DB para el organismo Pristionchus pacificus llamada Appa. DB. Gran parte de la funcionalidad de Ace. DB para C. elegans se ha puesto a disposición a través de la base de datos Worm. Base
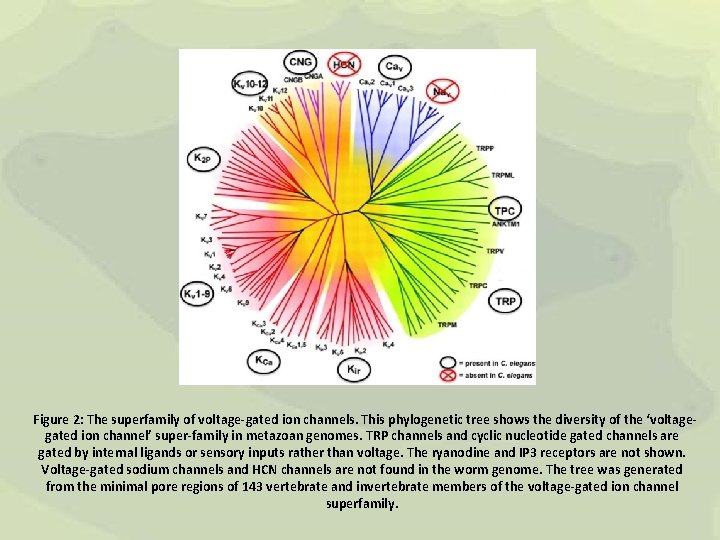
Figure 2: The superfamily of voltage-gated ion channels. This phylogenetic tree shows the diversity of the ‘voltagegated ion channel’ super-family in metazoan genomes. TRP channels and cyclic nucleotide gated channels are gated by internal ligands or sensory inputs rather than voltage. The ryanodine and IP 3 receptors are not shown. Voltage-gated sodium channels and HCN channels are not found in the worm genome. The tree was generated from the minimal pore regions of 143 vertebrate and invertebrate members of the voltage-gated ion channel superfamily.
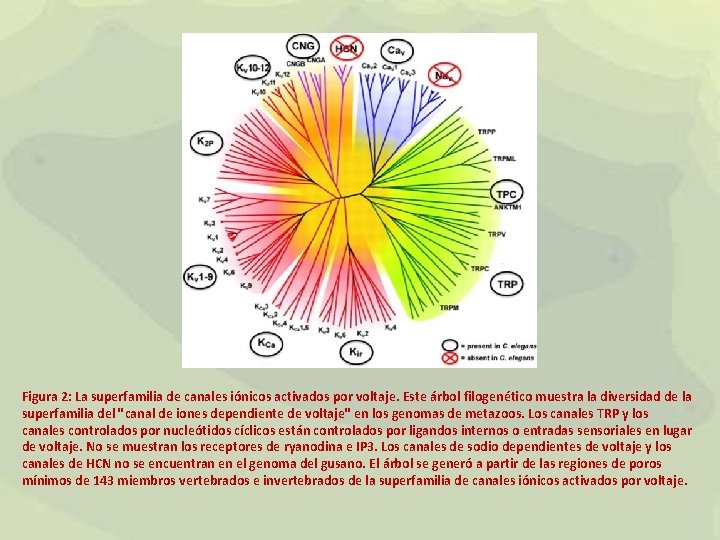
Figura 2: La superfamilia de canales iónicos activados por voltaje. Este árbol filogenético muestra la diversidad de la superfamilia del "canal de iones dependiente de voltaje" en los genomas de metazoos. Los canales TRP y los canales controlados por nucleótidos cíclicos están controlados por ligandos internos o entradas sensoriales en lugar de voltaje. No se muestran los receptores de ryanodina e IP 3. Los canales de sodio dependientes de voltaje y los canales de HCN no se encuentran en el genoma del gusano. El árbol se generó a partir de las regiones de poros mínimos de 143 miembros vertebrados e invertebrados de la superfamilia de canales iónicos activados por voltaje.

http: //www. wormbook. org/toc_signaltrans. html Worm. Book is a comprehensive, open-access collection of original, peer-reviewed chapters covering topics related to the biology of Caenorhabditis elegans and other nematodes. Wormbook also contains: Worm. Methods, a collection of protocols for nematode researchers; Worm. History, personal perspectives on C. elegans research; and the Worm Breeder's Gazette, an informal, non-refereed, biannual newsletter for the interchange of ideas and information related to C. elegans and other nematodes. Additional chapters can be found in GENETICS. Worm. Book es una colección completa de acceso abierto de capítulos originales revisados por pares que cubren temas relacionados con la biología de Caenorhabditis elegans y otros nematodos. Wormbook también contiene: Worm. Methods, una colección de protocolos para investigadores de nematodos; Worm. History, perspectivas personales sobre la investigación de C. elegans; y el Worm Breeder's Gazette, un boletín semestral informal, no arbitrado para el intercambio de ideas e información relacionada con C. elegans y otros nematodos. Se pueden encontrar capítulos adicionales en GENÉTICA.

Sources: : מקורות A brief introduction to C. elegans https: //youtu. be/zjq. Lw. Pg. Ln. V 0 Online Developmental Biology: Introduction to C. elegans https: //fineartamerica. com/art/c. +elegans https: //www. youtube. com/watch? v=zc 1 P 7 l. GSzd. U https: //twitter. com/ellie_elegans https: //www. genetics. org/content/203/1/35 https: //sketchfab. com/3 d-models/caenorhabditis-elegans https: //upload. wikimedia/Gastrulation_in_3 D. ogv איתי הרמן הפך מילד עם הפרעות קשב וריכוז לצ'ייסר שיודע הכל https: //www. youtube. com/watch? v=Ml. S 4 cb 90 UHY Clarita-Efraim pps: www. clarita-efraim. com chefetze@netvision. net. il
- Slides: 20