BOLILLA 11 Metabolismo del DNA Replicacin DNApolimerasas Fases

BOLILLA 11 • Metabolismo del DNA: Replicación. DNA-polimerasas. Fases de la Replicación. Reparación del DNA • Metabolismo del RNA: Transcripción. RNA-polimerasas. Iniciación y Terminación de la síntesis. Maduración del RNA • Transcriptasa inversa

ACIDOS NUCLEICOS • ü ü ü DNA: Acido desoxirribonucleico Contiene la información genética Está formado por dos cadenas polipeptídicas Se encuentra formando los cromosomas en el núcleo celular • RNA. Acido Ribonucleico ü Se encuentran 3 clases: 80%: ARNr ribosomal y 10 % ARNm mensajero en los ribosomas en citoplasma. Un 10 % ARNt transferencial. ü El ARNm posee la información génica para la síntesis de proteínas. ü Hay un 10% de ARN en nucleolos. ü Existen otros ARN: ARNnp ó sn. RNA y ARNcp ó sc. RNA
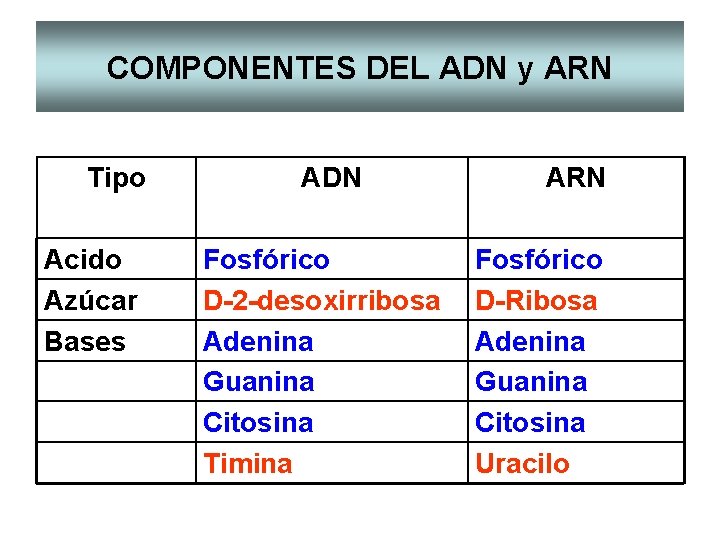
COMPONENTES DEL ADN y ARN Tipo Acido Azúcar Bases ADN Fosfórico D-2 -desoxirribosa Adenina Guanina Citosina Timina ARN Fosfórico D-Ribosa Adenina Guanina Citosina Uracilo
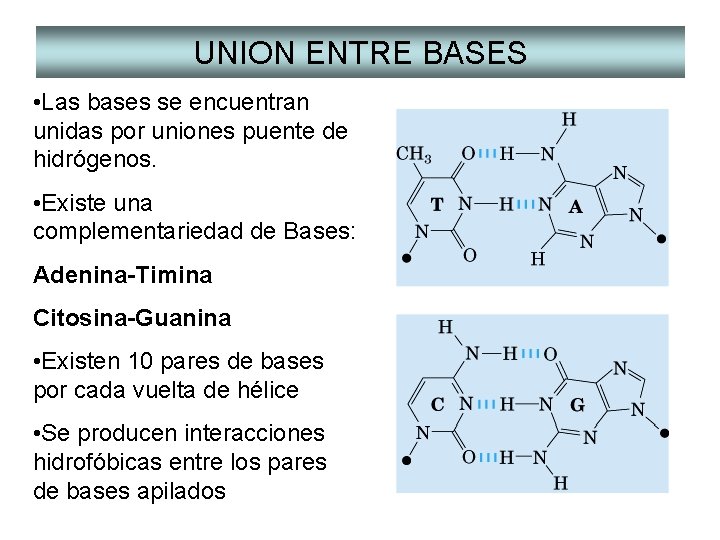
UNION ENTRE BASES • Las bases se encuentran unidas por uniones puente de hidrógenos. • Existe una complementariedad de Bases: Adenina-Timina Citosina-Guanina • Existen 10 pares de bases por cada vuelta de hélice • Se producen interacciones hidrofóbicas entre los pares de bases apilados
REPLICACION TRANSCRIPCION TRANSDUCCION RUTAS DE LA INFORMACION GENICA
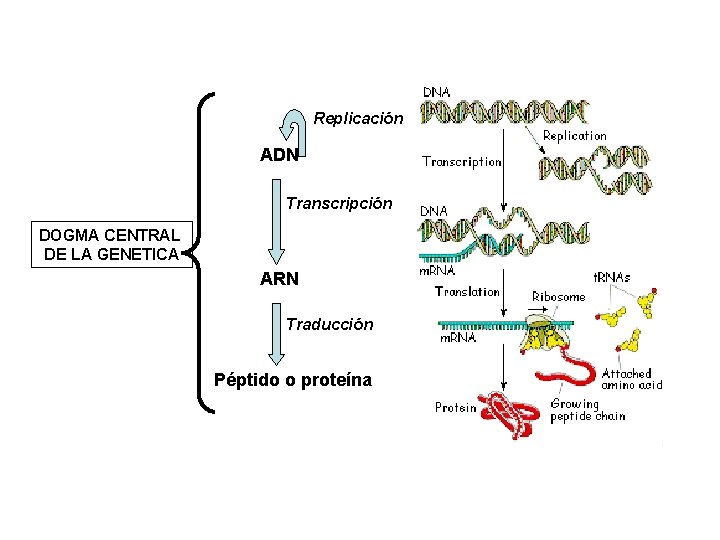
Replicación ADN Transcripción DOGMA CENTRAL DE LA GENETICA ARN Traducción Péptido o proteína

Acidos Nucleicos: Estructura molecular del ADN 1953. Watson, Crick y Wilkins 5’ 3’ Uniones Puente Hidrógeno 3’ 5’ - a-hélice con giro a la derecha. - Cadenas complementarias y antiparalelas. - Desoxinucleótidos de A, T, G, y C. - G-C 50% más fuerte que A-T.
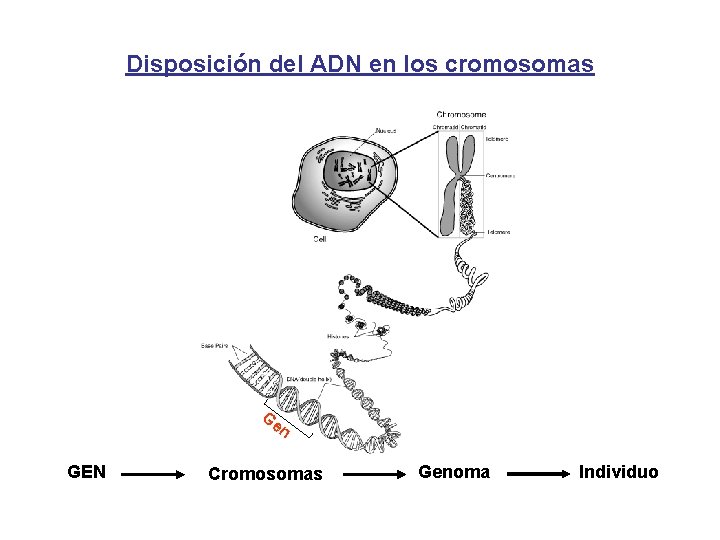
Disposición del ADN en los cromosomas Ge n GEN Cromosomas Genoma Individuo
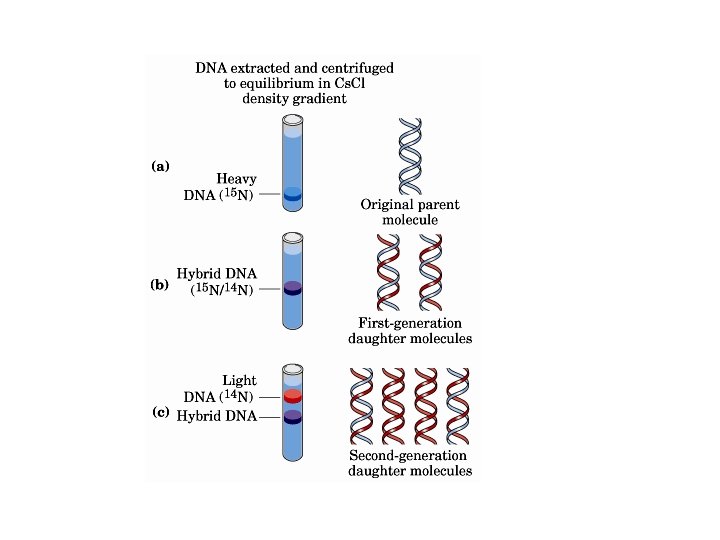
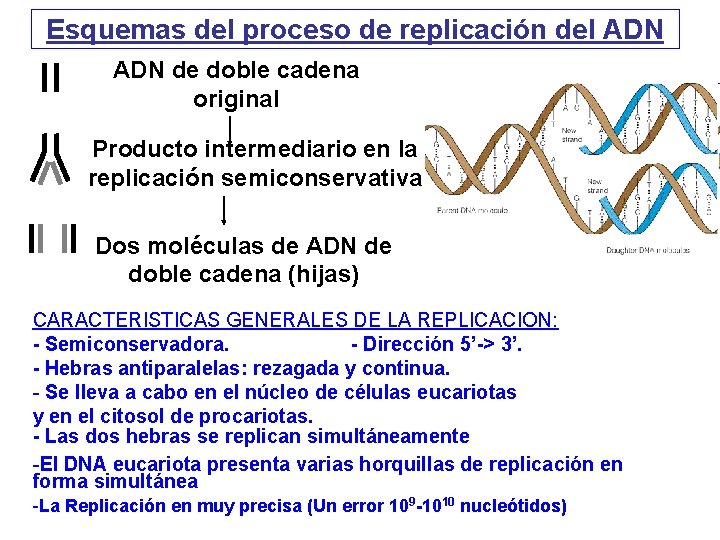
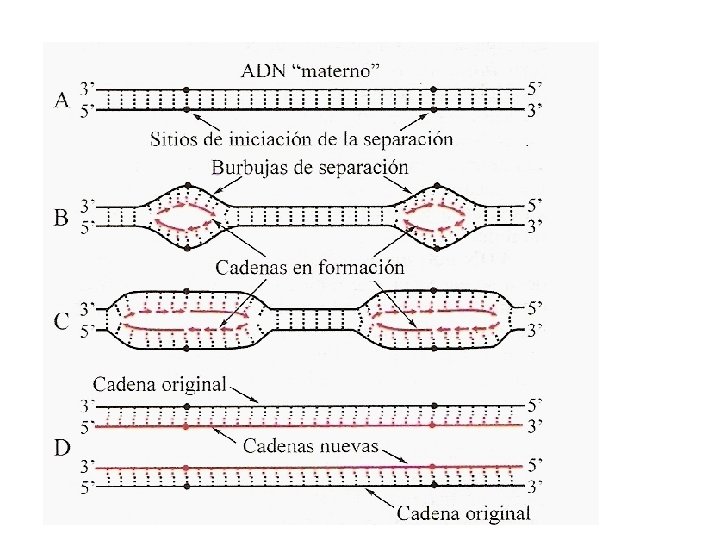
Esquemas del proceso de replicación del ADN de doble cadena original Producto intermediario en la replicación semiconservativa Dos moléculas de ADN de doble cadena (hijas) CARACTERISTICAS GENERALES DE LA REPLICACION: - Semiconservadora. - Dirección 5’-> 3’. - Hebras antiparalelas: rezagada y continua. - Se lleva a cabo en el núcleo de células eucariotas y en el citosol de procariotas. - Las dos hebras se replican simultáneamente -El DNA eucariota presenta varias horquillas de replicación en forma simultánea -La Replicación en muy precisa (Un error 109 -1010 nucleótidos)
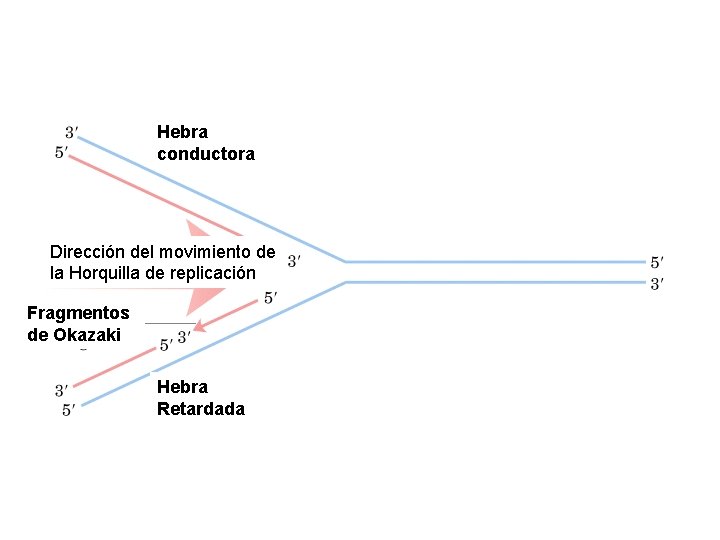
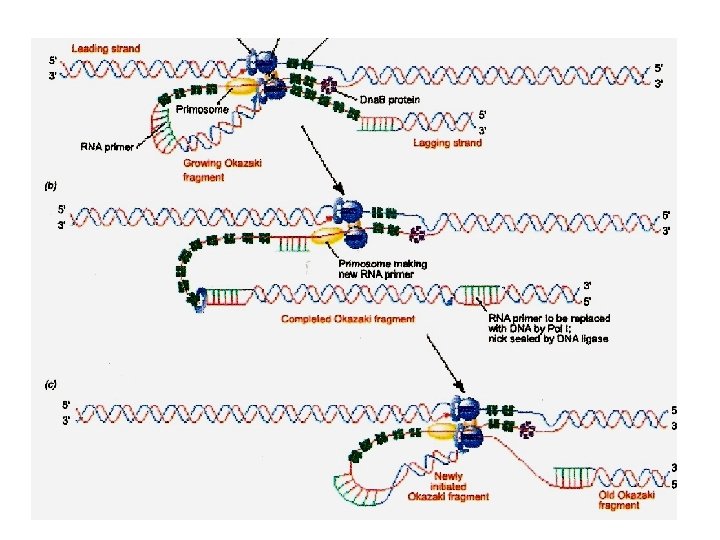
Hebra conductora Dirección del movimiento de la Horquilla de replicación Fragmentos de Okazaki Hebra Retardada
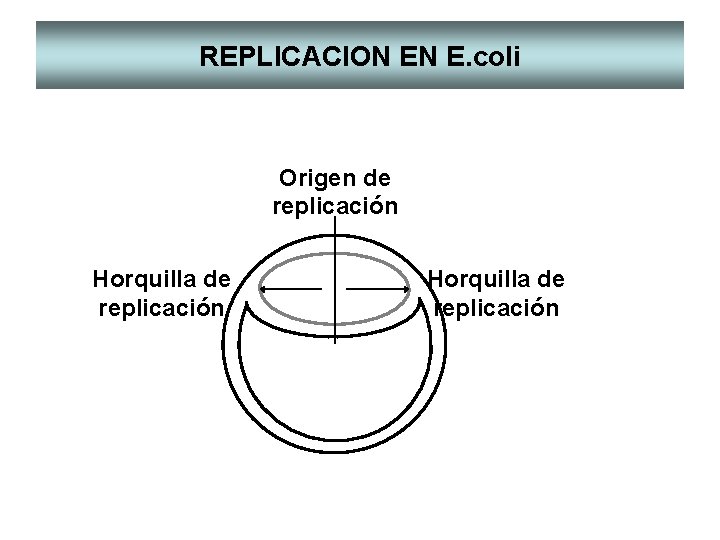
REPLICACION EN E. coli Origen de replicación Horquilla de replicación

Enzimas y cofactores que intervienen en la replicacion de ADN • • • DNA polimerasa: Catalizan la unión de d. RNT Proteína Dna. A: Reconoce la secuencia de origen Proteína Dna. B ó Helicasa: Desenrolla el DNA Primasa: Sintetiza cebadores DNA girasa ó Topoisomerasa II: Libera la tensión generada por el desenrollamiento del DNA • Proteínas fijadoras de ADN monocatenario: Mantienen las hebras separadas

ADN POLIMERASAS • Procariotas: Polimerasas I, II y III Polimerasa I: Actividad polimerasa y exonucleásica 3´ 5´ y 5´ 3´ Polimerasa II: Actividad polimerasa y exonucleásica 3´ 5´ Polimerasa III: Actividad polimerasa y exonucleásica 3´ 5´ • Eucariotas: Polimerasas a, b, g, d, e Polimerasa a: Actividad polimerasa (adiciona al inicio 20 d. NTP) Polimerasa b: Actúa en sistema de reparación de DNA Polimerasa d: Actividad polimerasa adiciona los restantes d. NTP) y exonucleásica 3´ 5´ Polimerasa g: DNA mitocondrial circular y actividad exonucleásica 3´ 5´ Polimerasa e: Actividad polimerasa y exonucleásica 3´ 5´
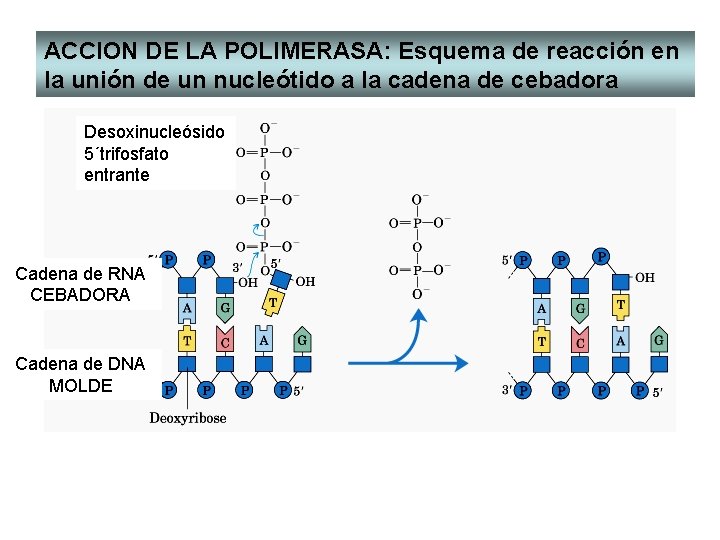
ACCION DE LA POLIMERASA: Esquema de reacción en la unión de un nucleótido a la cadena de cebadora Desoxinucleósido 5´trifosfato entrante Cadena de RNA CEBADORA Cadena de DNA MOLDE
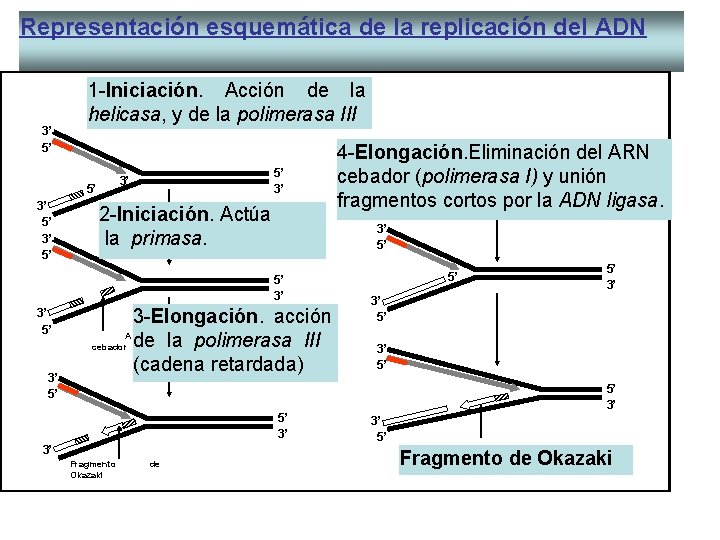
Representación esquemática de la replicación del ADN 3’ 5’ 1 -Iniciación. Acción de la helicasa, y de la polimerasa III 5’ 3’ 5’ 5’ 3’ 3’ 2 -Iniciación. Actúa la primasa. 3’ 5’ 5’ 3’ 3’ 5’ 3 -Elongación. acción ARN cebador de la polimerasa III (cadena retardada) 5’ 3’ 3’ Fragmento Okazaki de 4 -Elongación. Eliminación del ARN cebador (polimerasa I) y unión fragmentos cortos por la ADN ligasa. 5’ 5’ 3’ 3’ 5’ Fragmento de Okazaki

ESQUEMA BIOSINTESIS DE UN POLIMERO: Gasto de energÍa n d. ATP + n d. GTP + n d. TTP + n d. CTP • ADN polimerasa, Mg+ • ARN iniciador • Cadena molde Polímero 4 n d. RN + 4 n PPi Pirofosfatasa 2 Pi
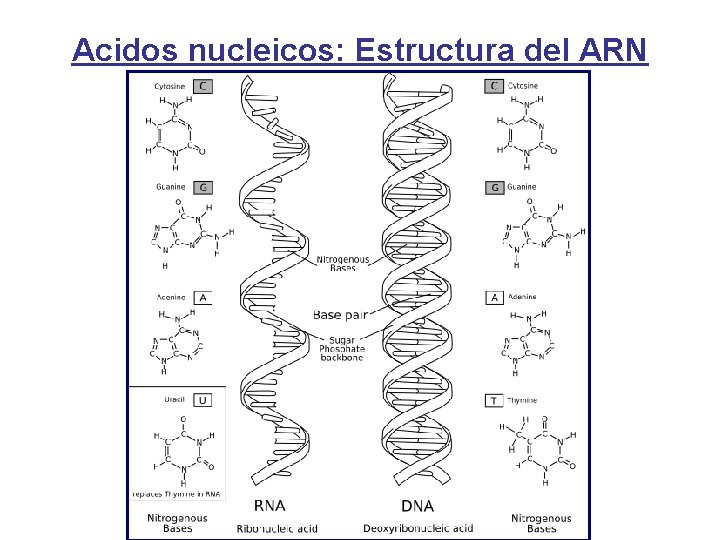
Acidos nucleicos: Estructura del ARN
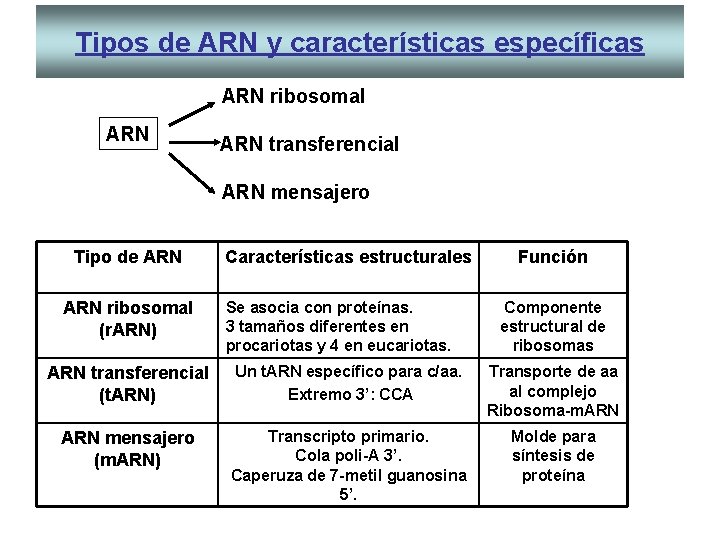
Tipos de ARN y características específicas ARN ribosomal ARN transferencial ARN mensajero Tipo de ARN ribosomal (r. ARN) Características estructurales Se asocia con proteínas. 3 tamaños diferentes en procariotas y 4 en eucariotas. Función Componente estructural de ribosomas ARN transferencial (t. ARN) Un t. ARN específico para c/aa. Extremo 3’: CCA Transporte de aa al complejo Ribosoma-m. ARN mensajero (m. ARN) Transcripto primario. Cola poli-A 3’. Caperuza de 7 -metil guanosina 5’. Molde para síntesis de proteína

TRANSCRIPCION O SINTESIS DE ARN • Actúa una ARN polimerasa dirigida por ADN • Utiliza los 4 ribonucleótidos: ATP, GTP, CTP y UTP. • Necesita Mg++ • Necesita ADN para su actividad • No requiere de un cebador • Se une a secuencias específicas (promotores) • El DNA se desenrolla y forma una burbuja de transcripción. • En eucariotas la polimerasa requiere de factores de transcripción.

ETAPAS DE LA TRANSCRIPCION O SINTESIS DE ARN • INICIO: Unión de la polimerasa al complejo y desenrollamiento del DNA • ELONGACION: Acción de la polimerasa y separación de la subunidad sigma. • TERMINACION: Disociación de la ARN polimerasa y liberación del transcripto
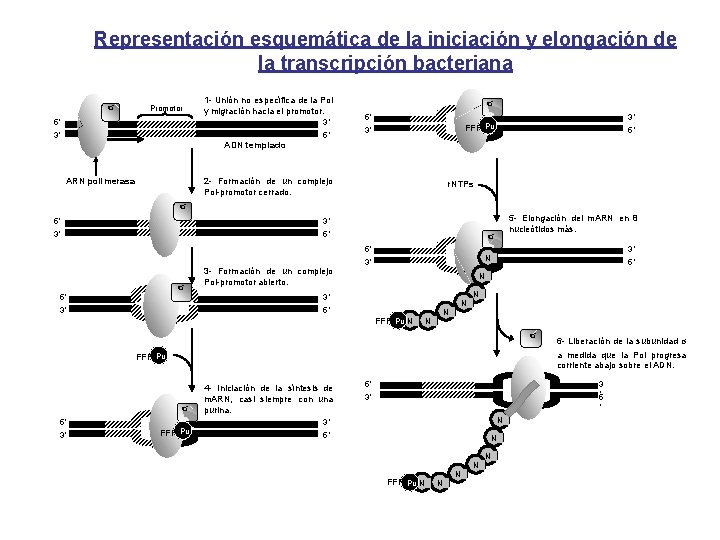
Representación esquemática de la iniciación y elongación de la transcripción bacteriana σ Promotor 1 - Unión no específica de la Pol y migración hacia el promotor. 5’ 3’ 3’ 5’ σ 5’ 3’ FFF Pu 3’ 5’ ADN templado ARN polimerasa 2 - Formación de un complejo Pol-promotor cerrado. r. NTPs σ 5’ 3’ 3’ 5’ σ 3 - Formación de un complejo Pol-promotor abierto. 5’ 3’ 3’ 5’ 5 - Elongación del m. ARN en 8 nucleótidos más. 3’ N 3’ 5’ N N N FFF Pu N N N σ a medida que la Pol progresa corriente abajo sobre el ADN. FFF Pu σ 5’ 3’ 6 - Liberación de la subunidad σ FFF Pu 4 - Iniciación de la síntesis de m. ARN, casi siempre con una purina. 3 ’ 5 5’ 3’ ’ N 3’ 5’ N N N FFF Pu N N N

MADURACION DEL ARN • En el extremo 5´ se adiciona un casquete de 7 -metil guanosina y en el 3´se forma la “cola” poli A. • Intervienen las ribozimas • Se eliminan secuencias no codificantes o intrones • Los exones se unen y forman una cadena única.
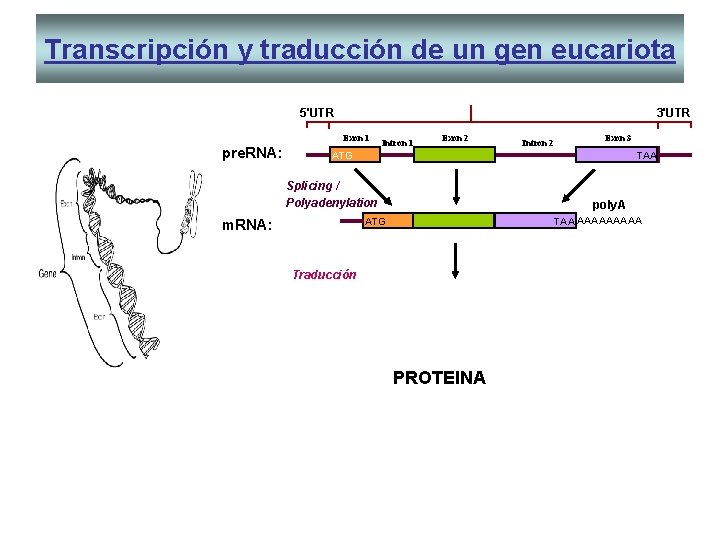
Transcripción y traducción de un gen eucariota 5'UTR 3'UTR Exon 1 pre. RNA: Intron 1 Exon 2 Exon 3 Intron 2 ATG TAA Splicing / Polyadenylation poly. A TAA AAAAA ATG m. RNA: Traducción active protein: CPLTW . . . GFL Splicing alternativo CPLTW . . . PJC PROTEINA Modificación posttransduccional CPLTW . . . LAC
- Slides: 26