BMP 5762 Bioinformtica Aplicada ao Estudo de Doenas

BMP 5762 – Bioinformática Aplicada ao Estudo de Doenças Parasitárias Prof Dr Arthur Gruber Instituto de Ciências Biológicas Metagenômica Carla Bartels Francisco M Ulloa Stanojlovic Luis Fábio Batista

• O termo Metagenômica foi usado primeiramente em 1998 por Jo Handelsman (Universidade de Wiscosin – EUA) Dr. Anand Kumar & Dr. R. A. Siddique

Introdução METAGENOMA É o genoma coletivo da microbiota total, encontrada em um determinado habitat. METAGENOMA METAGENÔMICA análise genômica de ÉÉoagenoma coletivodas dacomunidades microbiota total, microrganismos determinado ambiente por encontrada de emum um determinado habitat técnicas independentes de cultivo. Dr. Anand Kumar & Dr. R. A. Siddique
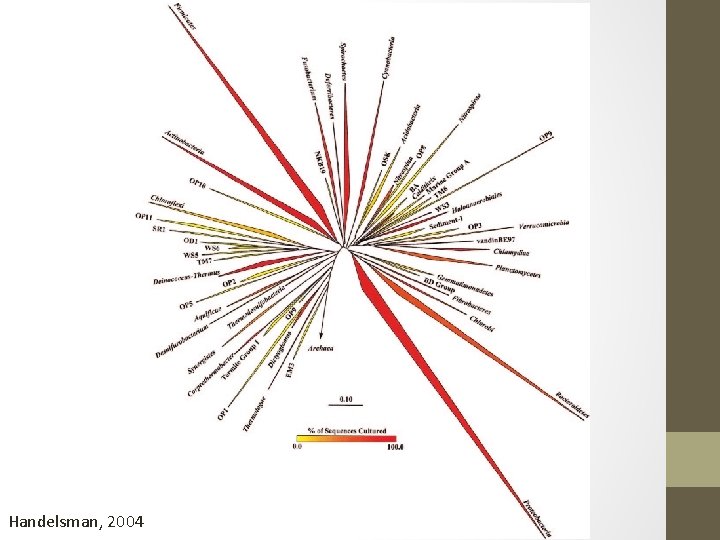
Handelsman, 2004
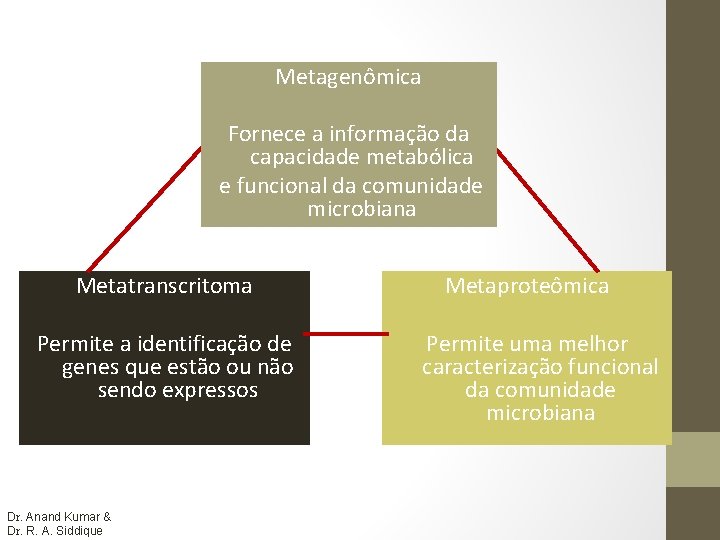
Metagenômica Fornece a informação da capacidade metabólica e funcional da comunidade microbiana Metatranscritoma Permite a identificação de genes que estão ou não sendo expressos Dr. Anand Kumar & Dr. R. A. Siddique Metaproteômica Permite uma melhor caracterização funcional da comunidade microbiana

Metagenômica aplicada Dr. Anand Kumar & Dr. R. A. Siddique

Metagenômica fornece Informação genética sobre possíveis novos biocatalizadores ou enzimas Conexões genômicas entre função e filogenia de organismos “não cultiváveis” Perfis evolutivos de função e estrutura de comunidades Novas hipóteses de funções microbiais Thomas et al, 2012

JCSetubal, 2012

JCSetubal, 2012

JCSetubal, 2012
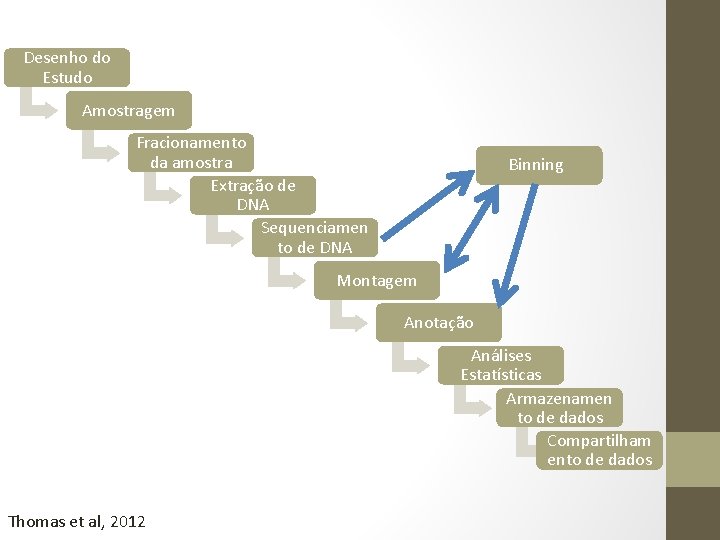
Desenho do Estudo Amostragem Fracionamento da amostra Extração de DNA Sequenciamen to de DNA Binning Montagem Anotação Análises Estatísticas Armazenamen to de dados Compartilham ento de dados Thomas et al, 2012
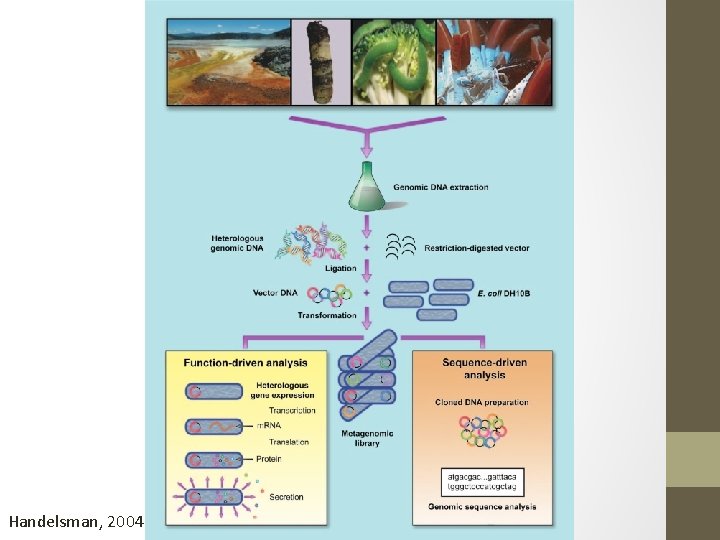
Handelsman, 2004
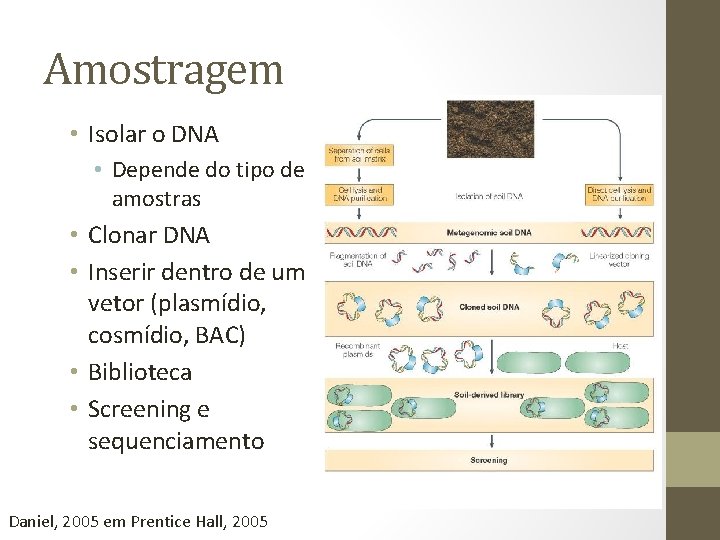
Amostragem • Isolar o DNA • Depende do tipo de amostras • Clonar DNA • Inserir dentro de um vetor (plasmídio, cosmídio, BAC) • Biblioteca • Screening e sequenciamento Daniel, 2005 em Prentice Hall, 2005

Amostragem {desafios} • Amostras devem representar a população → Quantas amostras são necessárias? Curvas de raridade para estimar fração de espécies sequenciadas. (Abundância x Complexidade). • Presença de populações dominantes afeta análises → representação maior e maior chance de montar contigs. • Quanto mais metadados forem coletados mais detalhadas serão as inferências das condições ambientais. Ex. : dados geográficos, bioquímicos, data de coleta, métodos de extração do DNA. Bruno Malveira Peixoto 2011
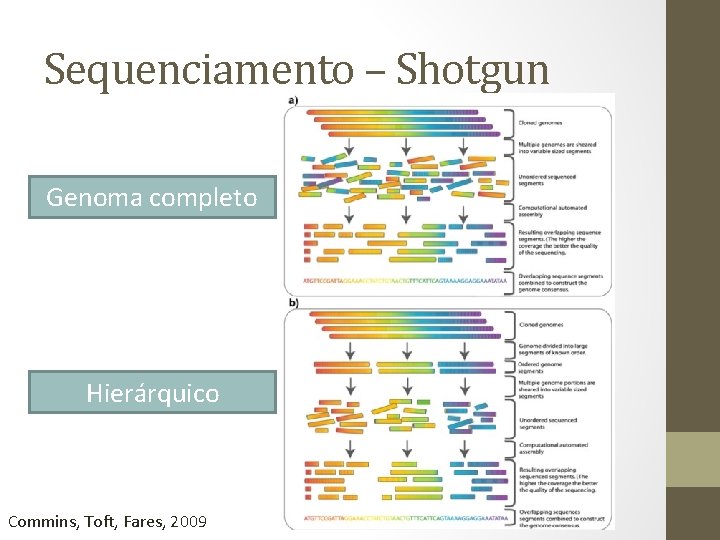
Sequenciamento – Shotgun Genoma completo Hierárquico Commins, Toft, Fares, 2009
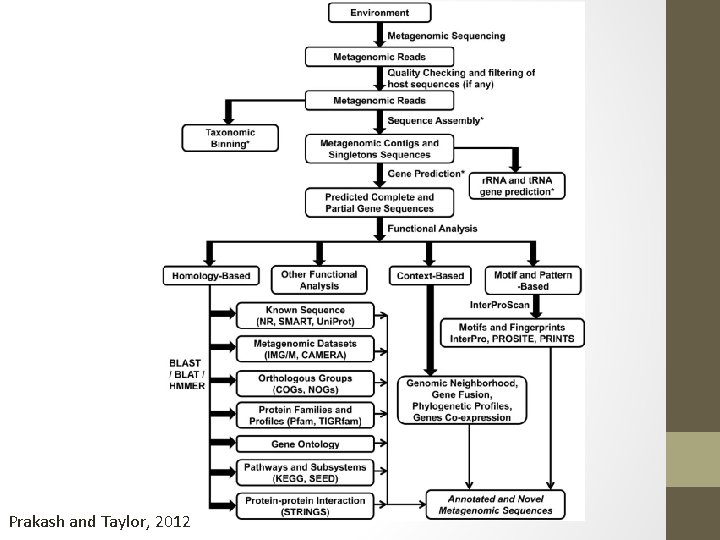
Prakash and Taylor, 2012

Montagem • Fatores a serem considerados: • Tamanho das leituras de sequenciamento usadas para criar a base de dados de metagenômica • São necessárias sequências mais longas para anotação? • A base de dados está montada para reduzir os requerimentos de processamento de dados?

Montagem baseada em referência: MIRA: An Automated Genome and Assembler ü Algoritmos rápidos rodam em laptop em 2 h; ü Regiões divergentes não são cobertas – inserções, deleções ou polimorfirmos. Montagem “de novo”: Velvet ü ü Meta-IDBA Meta. Velvet Baseados em gráficos de Bruijn Requer grandes recursos computacionais Requer milhares de gigabytes – dias. Meta-IDBA e Meta. Velvet – não clonalidade de populações naturais subgráficos de Bruijn - N 50 e tam. contig Thomas, Gilbert e Meyer, 2011

Montagem {limitações} • Amostragem incompleta – genomas parcialmente amostrados • Formação de quimeras – sequências de espécies diferentes • Dificuldade em montar amostras ricas em espécies (solo). Bruno Malveira Peixoto 2011

Métodos de Discriminação Processo de classificação das seqs de DNA em grupos que possam representar um genoma individual ou genomas de organismos fortemente relacionados Vários algoritmos foram desenvolvidos – empregam dois tipos de informações contidas dentro de uma dada seq DNA • Classificação composicional • Similaridade Pontos importantes a considerar: • Tipo de dado de entrada disponível • Existência de training datasets adequados ou genomas de referência • Algumas ferramentas combinam os dois approachs – Phymm. Bl, Meta. Cluster Thomas et al, 2012; Liu, 2012

Classificação Composicional • Genomas têm composição de nucleotídeos conservada e isto será refletido nos fragmentos de sequência dos genomas • Conteúdo de GC • Uso de códons • Sítios de reconhecimento – 5 S ou 16 S r. RNA • Bioinfo tools: • Phylopythia • S-GSCM • TACAO • Não funciona bem com leituras curtas por não conterem informações suficientes Thomas et al, 2012; Liu, 2012

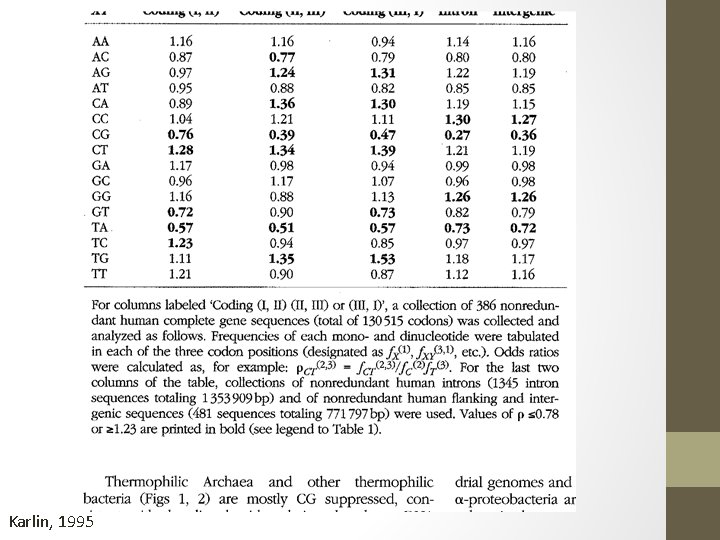
Conteúdo GC • Karlin & Burge, 1995 • A distribuição de nucleotídeos é relativamente constante dentro do genoma, mas varia entre genomas. • A razão de possibilidades (odds ratio) de frequência de conteúdo C+G é essencialmente a mesma na maioria dos organismos para todo o DNA versus o DNA codificante e também a mesma para as frações de DNA das diferentes sequências. • Talvez existam fatores que imponham limites às variações composicionais e estruturais de um genoma e que o conjunto de valores das odds ratios do dinucleotídeo seja uma assinatura genômica. • Diferenças significativas entre procariotos e eucariotos, entre vírus e seus hospedeiros. • Pxy = fxy / fx fy Karlin, 1995; Liu, 2012
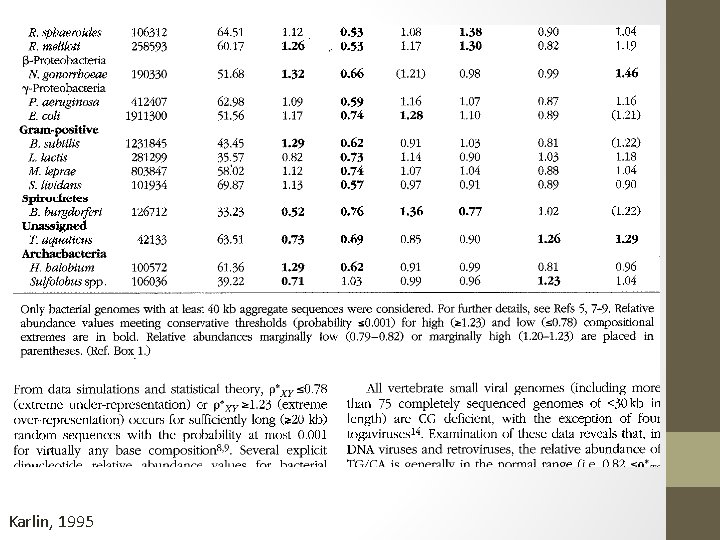
Karlin, 1995
Karlin, 1995
Uso de códons Todos os aminoácidos, exceto Met e Trp, são codificados por 2 a 6 códons Códons redundantes/sinônimos para qq aa não são usados com frequências iguais entre os diversos organismos Cada genoma tem uma estratégia particular de codificação Percentual de G+C na 3 a posição t. RNA do códon Codon Usage Database - http: //www. kazusa. or. jp/codon/ Karlin, 1998; Ikemura, 1985

Similaridade • Compara leituras curtas contra sequências codificadoras de bases de dados públicas de genes usando Blast. X e então designa para o seu ancestral comum mais tardio (LCA) de um organismo alvo • Bioinfo tools • • • IGG/M MG-RAST MEGAN CARMA Sort-ITEMS Meta. Phyler Thomas et al, 2012; Liu, 2012

Classificação {Bioinfo} • Análise de similaridade: IMG/M, MG-RAST, MEGAN, CARMA, Sort-ITEMS, Meta. Phyler • Análise composicional: Phylopythia, S-GSOM, PCAHIER, TACAO • Similaridade e composicional: Phymm. BL e Meta. Cluster Necessidade de sequências de referência* (marcador de RNAr) para fechar o alinhamento para sequenciamentos de leitura curta. * Base de dados escassas e tendenciosas para apenas três filos Proteobacteria, Firmicutes e Actinobacteria Bruno Malveira Peixoto 2011 Thomas, Gilbert e Meyer, 2011

ANÁLISES DOS DADOS • Dados de metagenômica cada vez mais abundantes necessitam de banco de dados para cobrir as informações taxonômicas e funcionais • Plataforma computacional robusta, combinado com programas de pesquisa de similaridade adaptados a esses dados.

Anotação • Contigs longos ≥ 30. 000 pb: RAST ou IMG • Contigs curtos Ø Fase 1: identificação dos genes: Frag. Gene. Scan (FGS) 1 -2% erro, Meta. Gene. Mark (MGM), Meta. Gene. Anotator (MGA), Metagene e Orphelia Ø Fase 2: identificação atribuição de função e agrupamento taxonômico
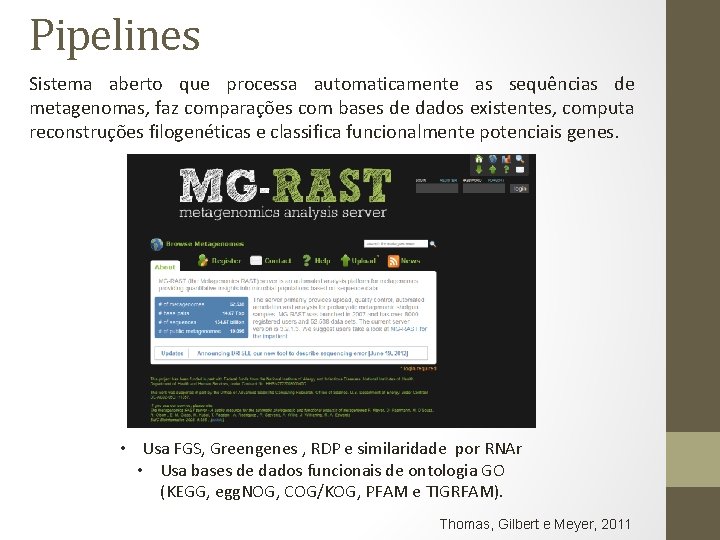
Pipelines Sistema aberto que processa automaticamente as sequências de metagenomas, faz comparações com bases de dados existentes, computa reconstruções filogenéticas e classifica funcionalmente potenciais genes. • Usa FGS, Greengenes , RDP e similaridade por RNAr • Usa bases de dados funcionais de ontologia GO (KEGG, egg. NOG, COG/KOG, PFAM e TIGRFAM). Thomas, Gilbert e Meyer, 2011
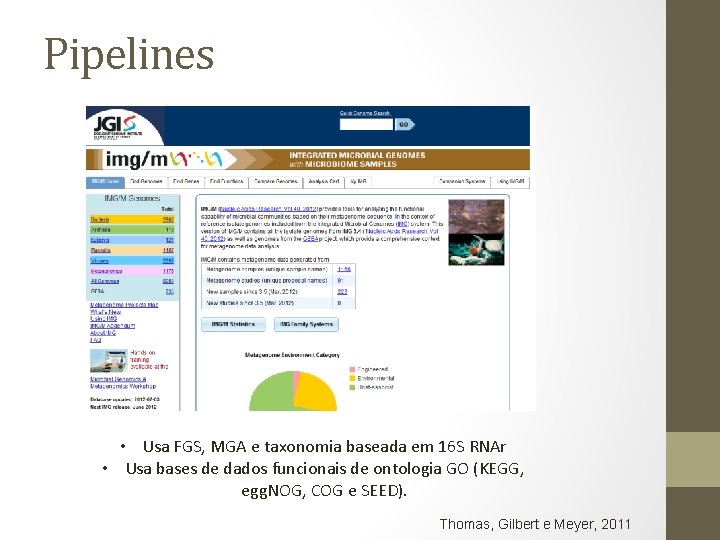
Pipelines • Usa FGS, MGA e taxonomia baseada em 16 S RNAr • Usa bases de dados funcionais de ontologia GO (KEGG, egg. NOG, COG e SEED). Thomas, Gilbert e Meyer, 2011

Pipelines • Usa FGA e MGA • Oferece esquema de anotação mais flexível • Requer o uso do mesmo workflow para análise Thomas, Gilbert e Meyer, 2011

Pipelines MEGAN

Aplicações

Aplicações o. Identificar genes funcionais e/ou novas vias metabólicas o. Estimar a diversidade microbiana; permitindo o estudo dos genomas em uma comunidade como um todo o. Compreender a dinâmica da população de uma comunidade inteira.

üSaúde
ü Bioenergia

üMetabolismo animal

üIdentificação novos patógenos

üVigilância

üMedicina forense
BIOPROSPECÇÃO FUNCIONAL SEQUÊNCIAS

BIOPROSPECÇÃO

ESTUDOS ECOLÓGICOS Primeiros estudos • Mar de Sargaços – Comunidade complexa – Genes desconhecidos – Filotipos novos – Impossibilidade de sequenciar todos os genomas presentes na amostra
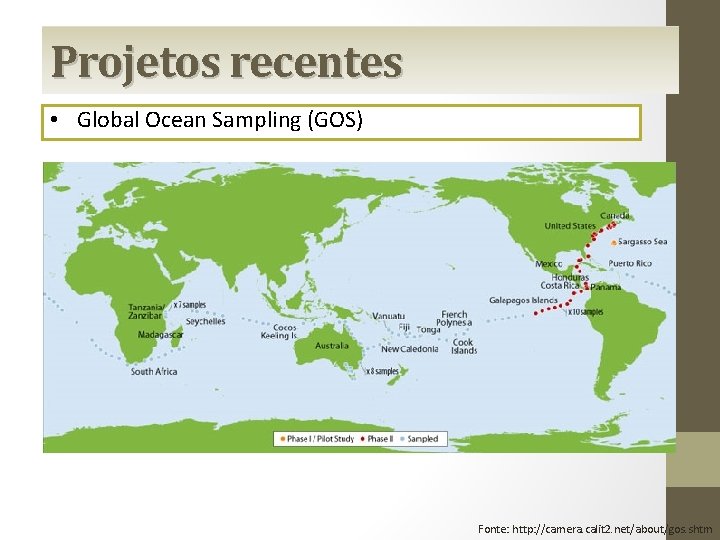
Projetos recentes • Global Ocean Sampling (GOS) Fonte: http: //camera. calit 2. net/about/gos. shtm

• Microorganismos representam mais de 90% da biomassa do oceano, mediam todos os ciclos bioquímicos nos oceanos e são responsáveis por 98% da produção primária no mar. Metagenômica é uma abordagem inovadora de sequenciação para examinar as espécies microbianas de espaço aberto sem a necessidade de isolamento e cultura de laboratório de espécies individuais. Alves, 2007

Projetos recentes
Projetos recentes
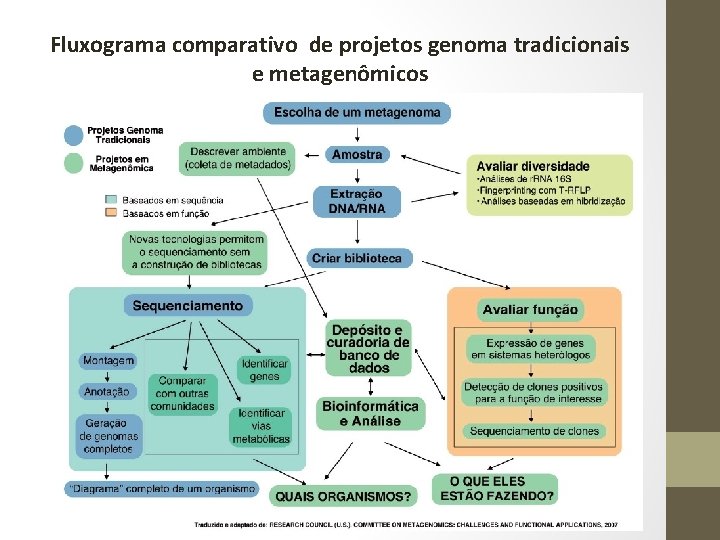
Fluxograma comparativo de projetos genoma tradicionais e metagenômicos

OBRIGADO!
- Slides: 50