BLAST en el NCBI BLAST en el NCBI

BLAST en el NCBI

BLAST en el NCBI Basic Local Alignment Search Tool Es la herramienta más importante de la Bioinformática porque: 1. - La comparación de una secuencia desconocida con las de una BD permite hacer anotaciones 2. - Es un método rápido 3. - Es un método fiable, tanto por la solidez de su análisis estadístico como por el grado de desarrollo del software 4. - Es un método flexible, que permite comparar secuencias en múltiples escenarios 5. - Es una herramienta consolidada y de uso generalizado, ya que cualquier persona con un ordenador conectado a Internet la puede utilizar Características de la herramienta BLAST

BLAST en el NCBI Aplicaciones de BLAST
BLAST en el NCBI ID - Mapping – Exploring Aplicaciones de BLAST

BLAST en el NCBI https: //blast. ncbi. nlm. nih. gov/Blast. cgi Página principal de BLAST (NCBI)

BLAST en el NCBI “Standalone BLAST” es un programa que te puedes descargar para instalarlo en tu ordenador y usarlo sin conexión a Internet. También te tienes que descargar las BD. Búsquedas especializadas con BLAST (NCBI)

BLAST en el NCBI BLAST compara una secuencia problema (query sequence) de nucleótidos o de proteínas con todas las secuencias de una BD para encontrar regiones de similitud local. Al mismo tiempo calcula la significancia estadística de cada resultado. Permite inferir relaciones funcionales y evolutivas, así como identificar miembros de una familia de genes o de proteínas. ¿ Qué hace BLAST ?
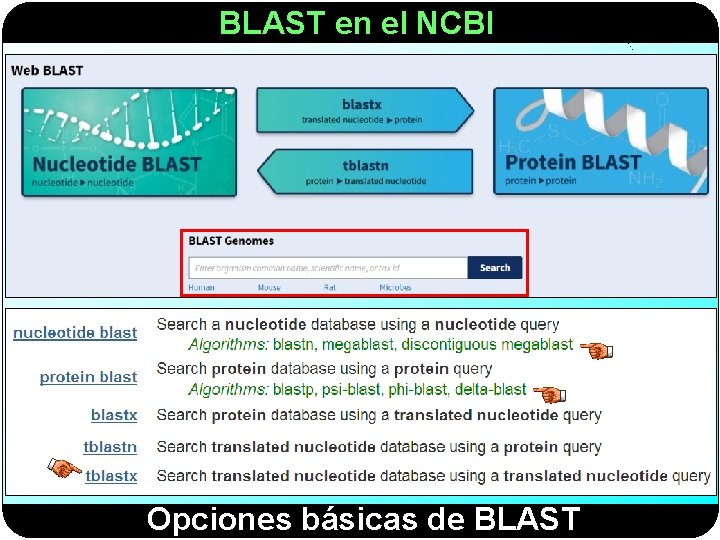
BLAST en el NCBI Opciones básicas de BLAST
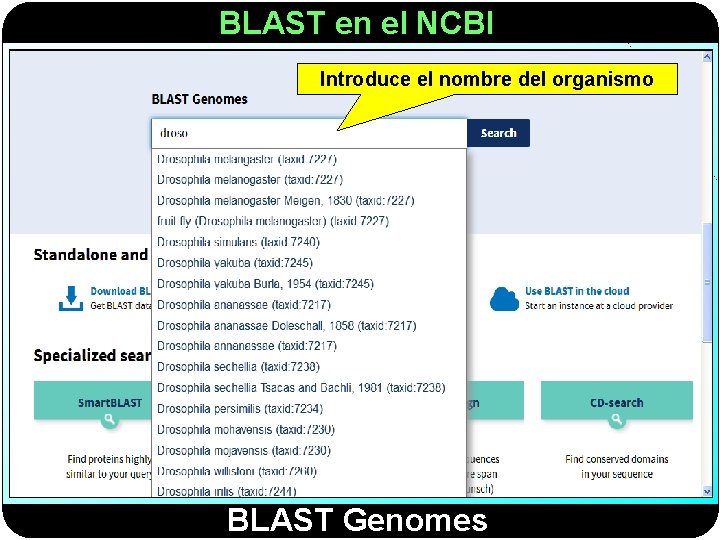
BLAST en el NCBI Introduce el nombre del organismo BLAST Genomes

BLAST en el NCBI Para hacer una búsqueda con BLAST (NCBI) 1. - https: //blast. ncbi. nlm. nih. gov/Blast. cgi 2. - Escoge una versión del programa BLAST 3. - Introduce la secuencia problema 4. - Selecciona una base de datos 5. - Selecciona un organismo 6. - Selecciona el algoritmo adecuado a la búsqueda 7. - Selecciona los parámetros de la búsqueda 8. - ¡BLAST! 9. - Analiza los resultados como si se tratase de un experimento ¿ Cómo se hace una búsqueda con BLAST ?
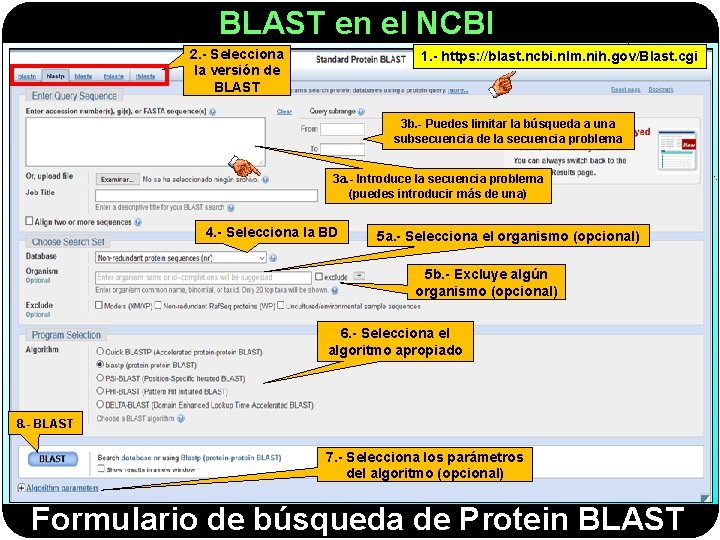
BLAST en el NCBI 2. - Selecciona la versión de BLAST 1. - https: //blast. ncbi. nlm. nih. gov/Blast. cgi 3 b. - Puedes limitar la búsqueda a una subsecuencia de la secuencia problema 3 a. - Introduce la secuencia problema (puedes introducir más de una) 4. - Selecciona la BD 5 a. - Selecciona el organismo (opcional) 5 b. - Excluye algún organismo (opcional) 6. - Selecciona el algoritmo apropiado 8. - BLAST 7. - Selecciona los parámetros del algoritmo (opcional) Formulario de búsqueda de Protein BLAST
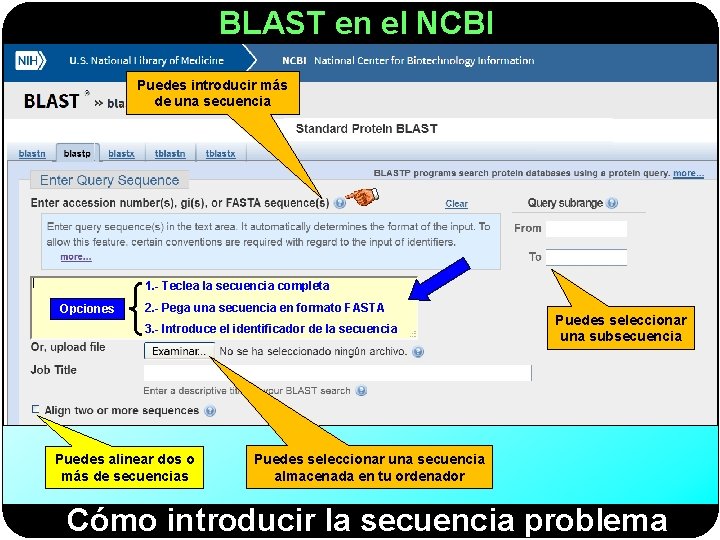
BLAST en el NCBI Puedes introducir más de una secuencia 1. - Teclea la secuencia completa Opciones 2. - Pega una secuencia en formato FASTA 3. - Introduce el identificador de la secuencia Puedes alinear dos o más de secuencias Puedes seleccionar una subsecuencia Puedes seleccionar una secuencia almacenada en tu ordenador Cómo introducir la secuencia problema
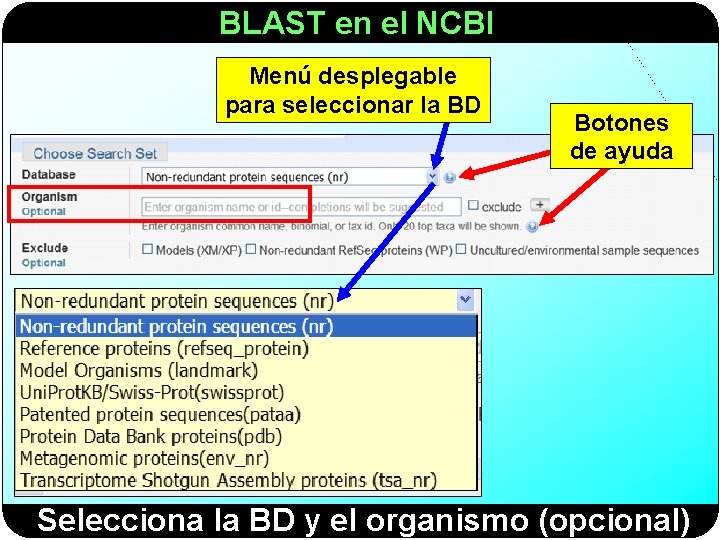
BLAST en el NCBI Menú desplegable para seleccionar la BD Botones de ayuda Selecciona la BD y el organismo (opcional)
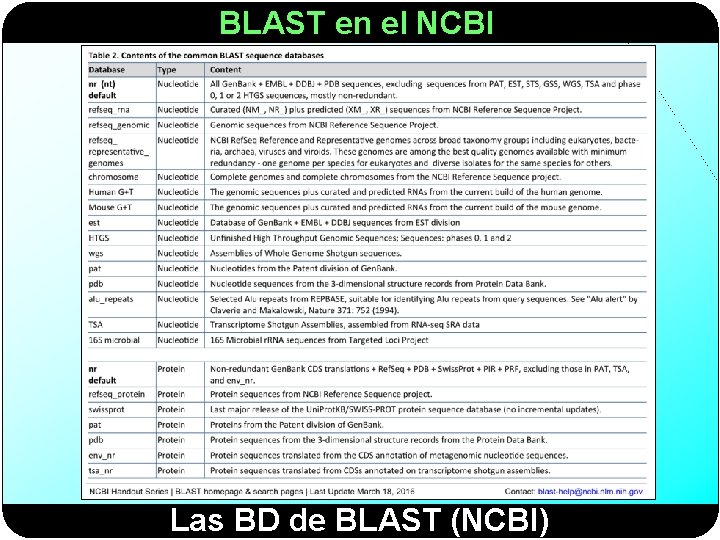
BLAST en el NCBI Las BD de BLAST (NCBI)

BLAST en el NCBI Selecciona el algoritmo adecuado
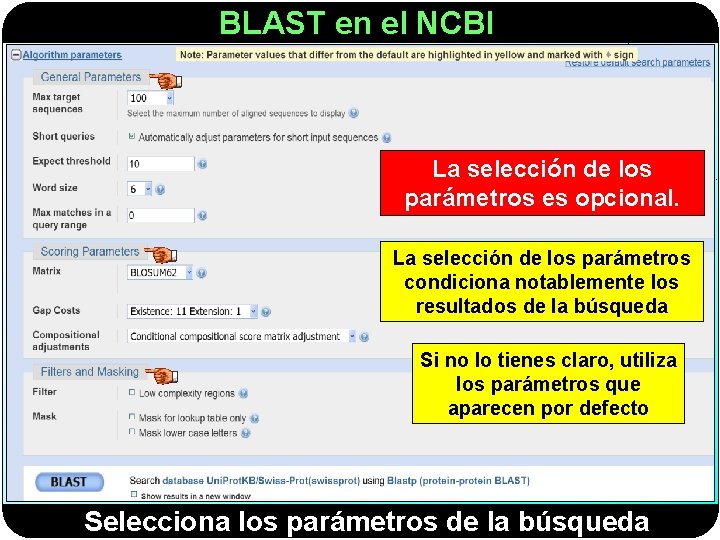
BLAST en el NCBI La selección de los parámetros es opcional. La selección de los parámetros condiciona notablemente los resultados de la búsqueda Si no lo tienes claro, utiliza los parámetros que aparecen por defecto Selecciona los parámetros de la búsqueda
BLAST en el NCBI Inicia la búsqueda
BLAST en el NCBI La búsqueda se está realizando…
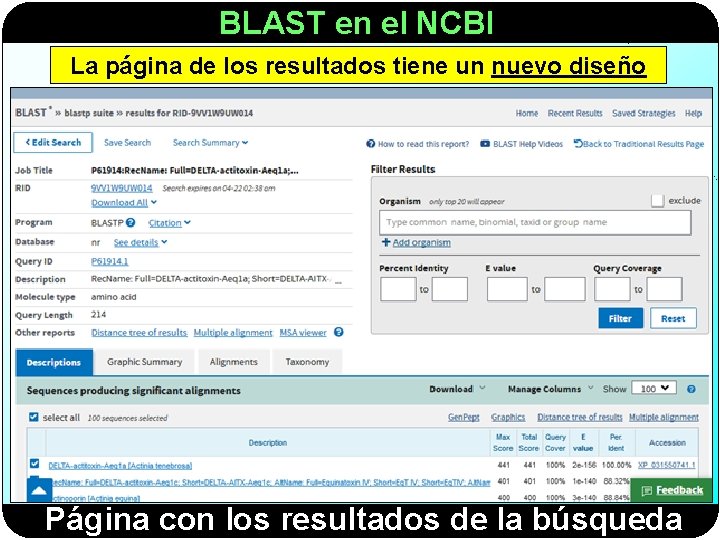
BLAST en el NCBI La página de los resultados tiene un nuevo diseño Página con los resultados de la búsqueda
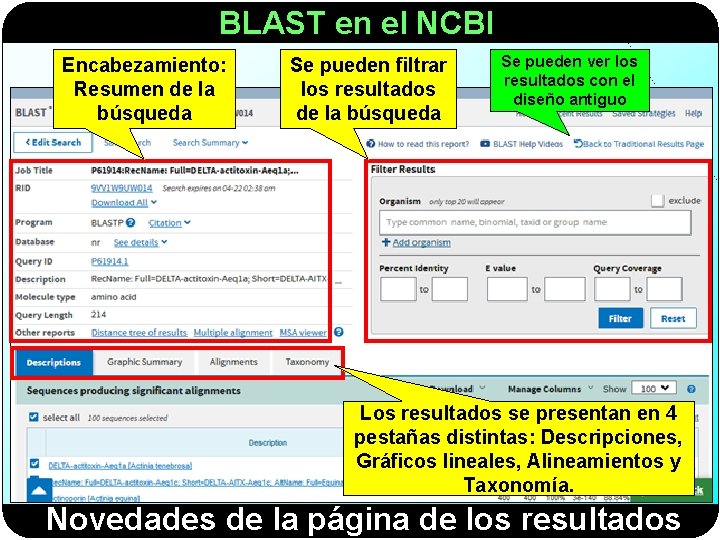
BLAST en el NCBI Encabezamiento: Resumen de la búsqueda Se pueden filtrar los resultados de la búsqueda Se pueden ver los resultados con el diseño antiguo Los resultados se presentan en 4 pestañas distintas: Descripciones, Gráficos lineales, Alineamientos y Taxonomía. Novedades de la página de los resultados
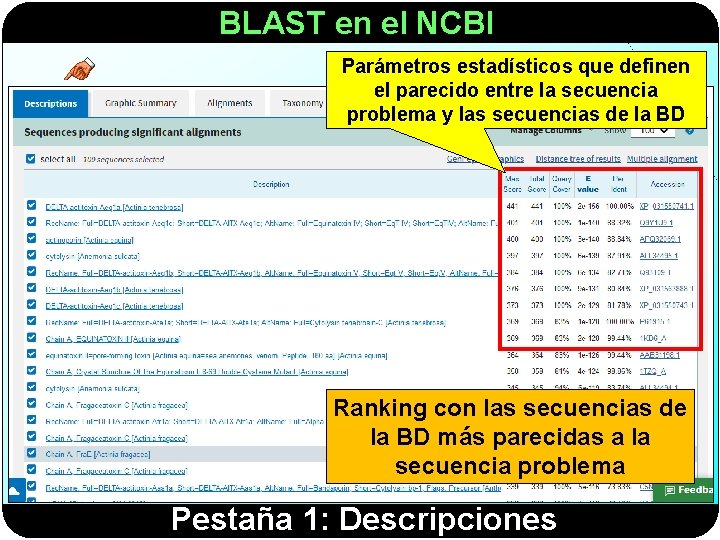
BLAST en el NCBI Parámetros estadísticos que definen el parecido entre la secuencia problema y las secuencias de la BD Ranking con las secuencias de la BD más parecidas a la secuencia problema Pestaña 1: Descripciones
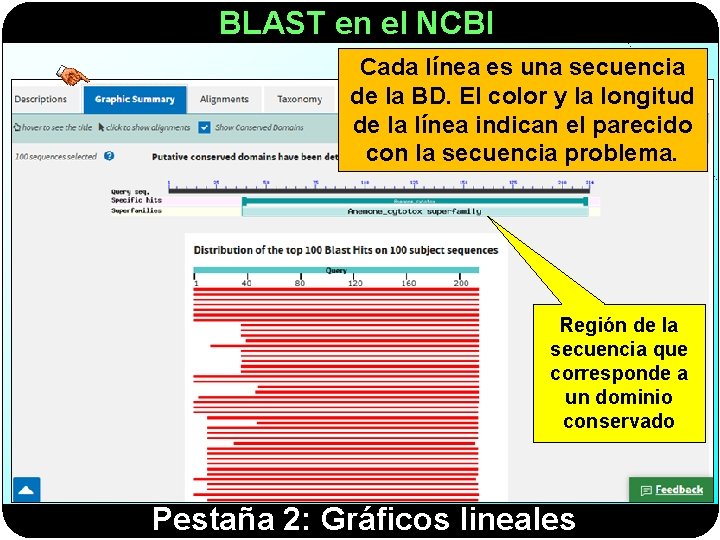
BLAST en el NCBI Cada línea es una secuencia de la BD. El color y la longitud de la línea indican el parecido con la secuencia problema. Región de la secuencia que corresponde a un dominio conservado Pestaña 2: Gráficos lineales
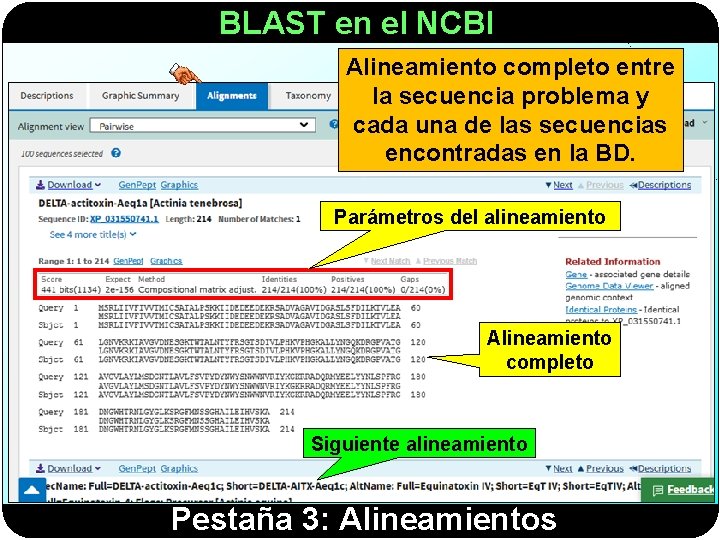
BLAST en el NCBI Alineamiento completo entre la secuencia problema y cada una de las secuencias encontradas en la BD. Parámetros del alineamiento Alineamiento completo Siguiente alineamiento Pestaña 3: Alineamientos

BLAST en el NCBI Datos taxonómicos de las especies a las que pertenecen las secuencias encontradas en la BD. Pestaña 4: Taxonomía
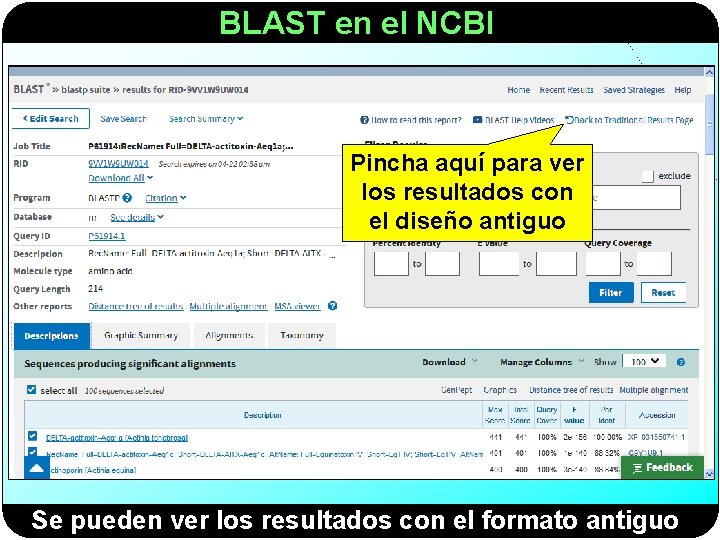
BLAST en el NCBI Pincha aquí para ver los resultados con el diseño antiguo Se pueden ver los resultados con el formato antiguo
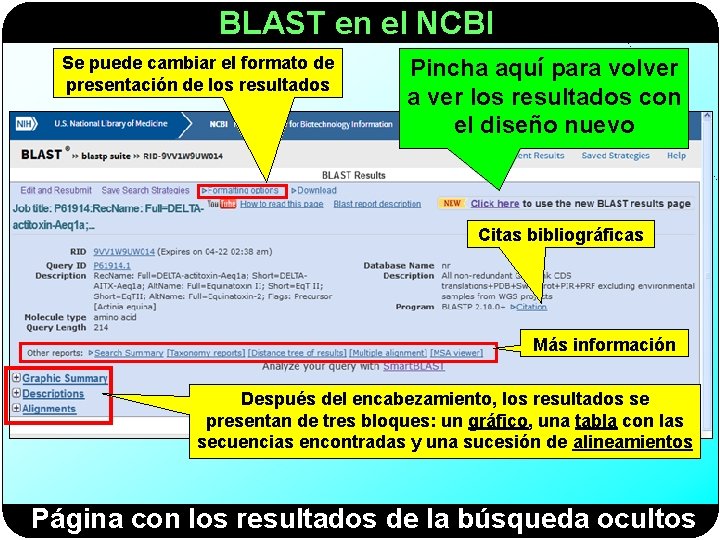
BLAST en el NCBI Se puede cambiar el formato de presentación de los resultados Pincha aquí para volver a ver los resultados con el diseño nuevo Citas bibliográficas Más información Después del encabezamiento, los resultados se presentan de tres bloques: un gráfico, una tabla con las secuencias encontradas y una sucesión de alineamientos Página con los resultados de la búsqueda ocultos
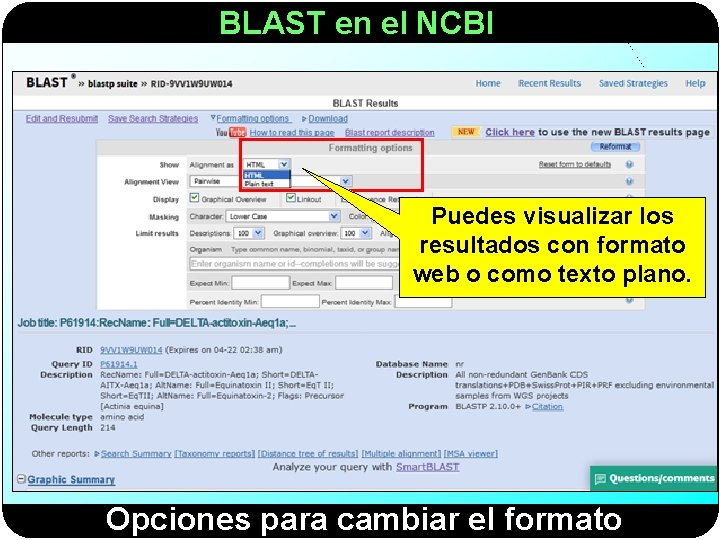
BLAST en el NCBI Puedes visualizar los resultados con formato web o como texto plano. Opciones para cambiar el formato
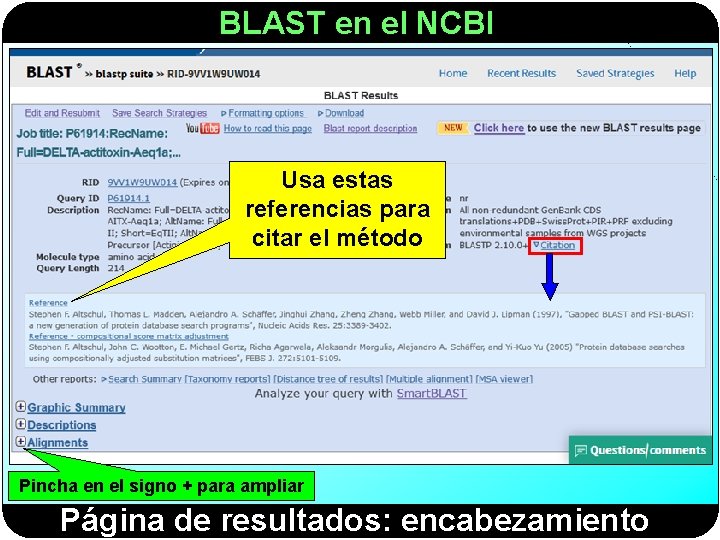
BLAST en el NCBI Usa estas referencias para citar el método Pincha en el signo + para ampliar Página de resultados: encabezamiento
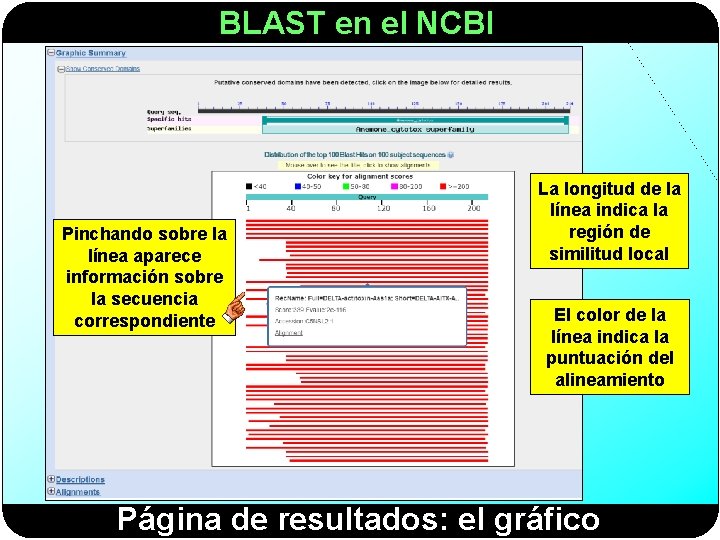
BLAST en el NCBI Pinchando sobre la línea aparece información sobre la secuencia correspondiente La longitud de la línea indica la región de similitud local El color de la línea indica la puntuación del alineamiento Página de resultados: el gráfico
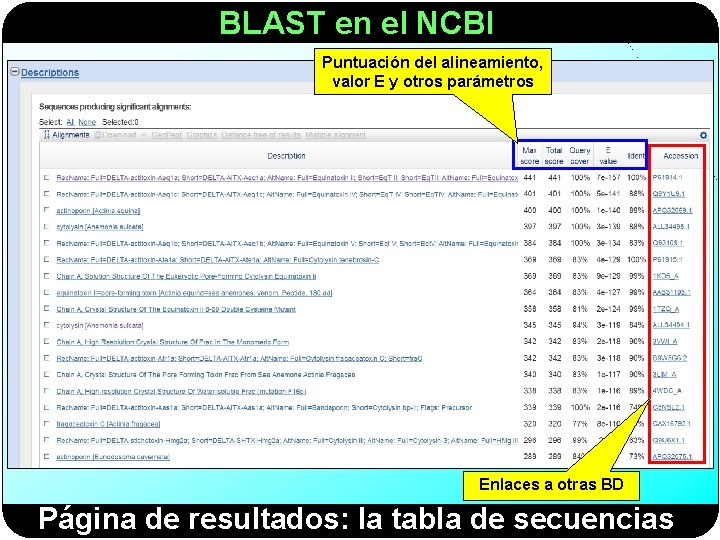
BLAST en el NCBI Puntuación del alineamiento, valor E y otros parámetros Enlaces a otras BD Página de resultados: la tabla de secuencias

BLAST en el NCBI http: //www. ncbi. nlm. nih. gov/BLAST/tutorial/Altschul-1. html La estadística que hay detrás de BLAST

BLAST en el NCBI El valor E
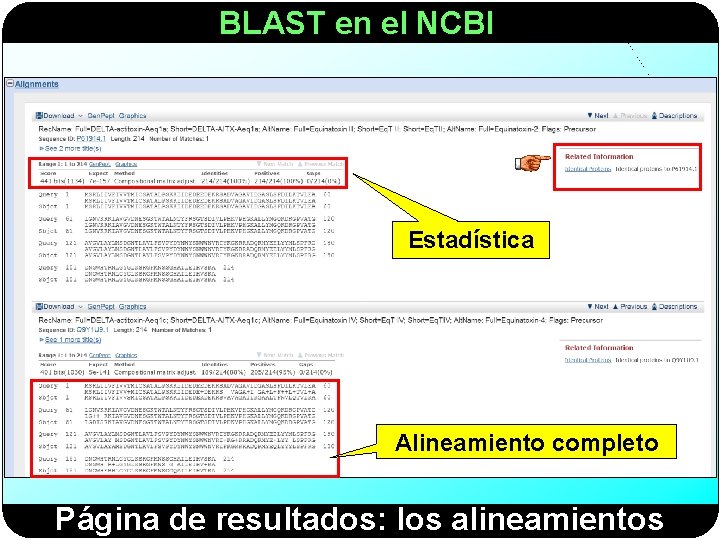
BLAST en el NCBI Estadística Alineamiento completo Página de resultados: los alineamientos
BLAST en el NCBI API BLAST: Puedes incorporar la herramienta BLAST en tu propia aplicación bioinformática. Si quieres trabajar sin estar conectado a Internet (para preservar la confidencialidad de los datos), puedes descargarte el programa y las BD para instalarlos en un ordenador personal. Puedes descargar gratuitamente el programa y las BD de BLAST
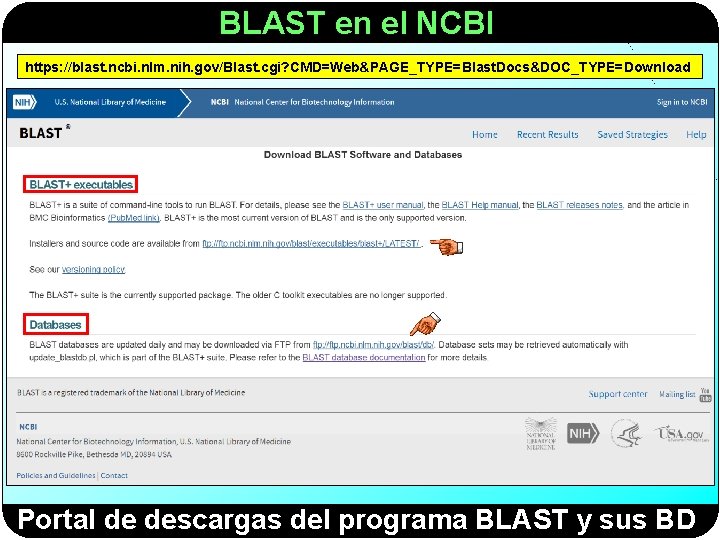
BLAST en el NCBI https: //blast. ncbi. nlm. nih. gov/Blast. cgi? CMD=Web&PAGE_TYPE=Blast. Docs&DOC_TYPE=Download Portal de descargas del programa BLAST y sus BD

BLAST en el NCBI ftp: //ftp. ncbi. nlm. nih. gov/blast/executables/blast+/LATEST/ Directorio de descargas del programa BLAST

BLAST en el NCBI ftp: //ftp. ncbi. nlm. nih. gov/blast/db/ Directorio de descargas de las BD de BLAST
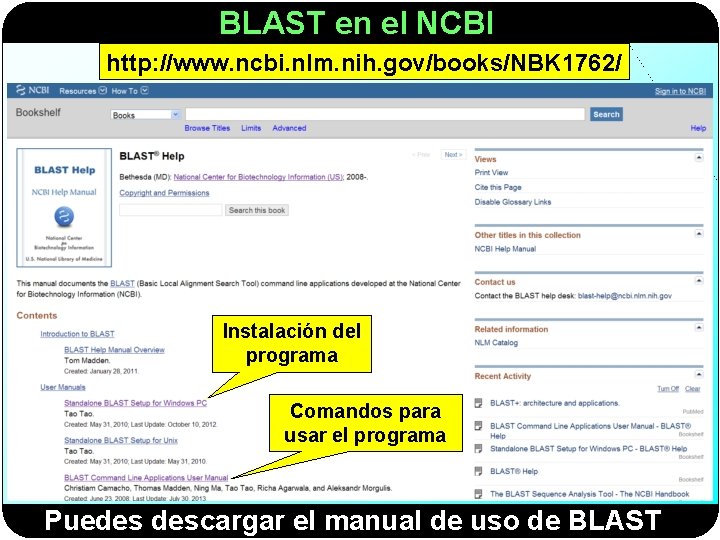
BLAST en el NCBI http: //www. ncbi. nlm. nih. gov/books/NBK 1762/ Instalación del programa Comandos para usar el programa Puedes descargar el manual de uso de BLAST

BLAST en el NCBI

BLAST en el NCBI (Protein) Versiones básicas de BLAST (1)

BLAST en el NCBI Versiones básicas de BLAST (2)
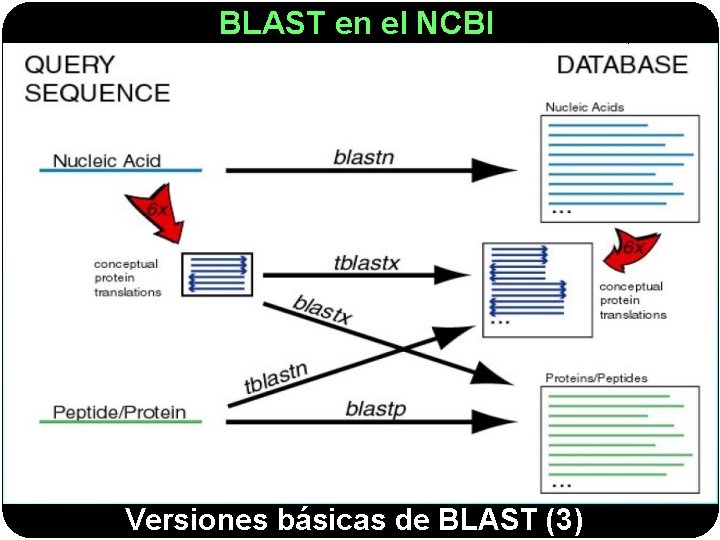
BLAST en el NCBI Versiones básicas de BLAST (3)

BLAST en el NCBI Hay tres buenas razones para comparar secuencias a nivel de proteína en vez de a nivel de nucleótidos: 1. - El código genético está degenerado: secuencias de nucleótidos aparentemente muy distintas pueden codificar la misma proteína. 2. - Las secuencias de proteínas contienen más información (4, 32 bits por residuo) que las secuencias de nucleótidos (2 bits por residuo). Esto implica que con secuencias proteicas se pueden obtener resultados significativos con alineamientos más cortos. 3. - Las matrices de sustitución (PAM, BLOSUM) utilizadas para puntuar alineamientos de proteínas son mucho más sofisticadas que las utilizadas para alinear nucleótidos y reflejan mucho mejor la similitud biológica entre dos secuencias. Lógicamente, las secuencias no codificantes sólo se pueden comparar a nivel de nucleótidos. ¿Para qué traducir las secuencias de nucleótidos?

BLAST en el NCBI
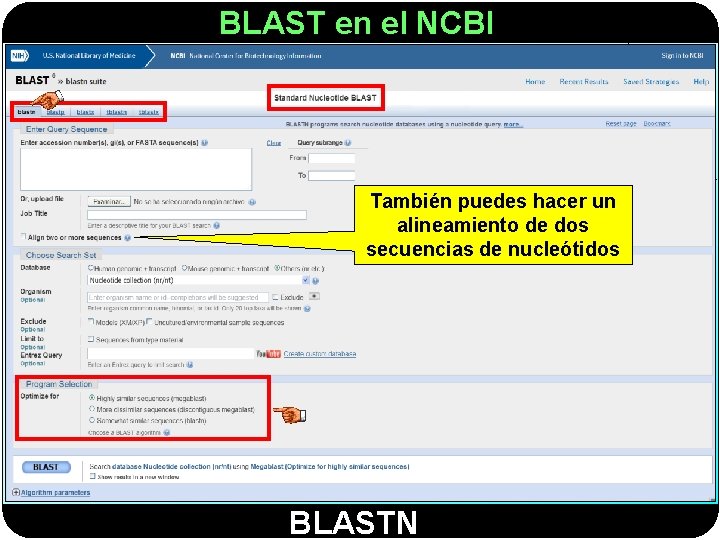
BLAST en el NCBI También puedes hacer un alineamiento de dos secuencias de nucleótidos BLASTN

BLAST en el NCBI Los distintos algoritmos de BLASTN

BLAST en el NCBI Se suele utilizar para: 1. - Localizar en un genoma oligonucleótidos, ADNc, EST, productos de PCR o elementos repetitivos 2. - Identificación de secuencias de ADN y anotación del ADN genómico 3. - Localizar secuencias homólogas en otras especies (genes de ARN o proteínas, regiones reguladoras, etc. ) 4. - Generación de contigs a partir de las lecturas cortas obtenidas durante la secuenciación 5. - Eliminar subsecuencias pertenecientes a vectores 6. - Detectar otros tipos de contaminación Usos de BLASTN

BLAST en el NCBI When a query sequence is searched against a database, both strands of the query are examined. The plus strand is the sequence in the FASTA file. The minus strand is the reverse complement of this sequence. If the similarity between the query and subject sequences is on the same strand, both sequences are labeled as being on the plus strand the coordinates increase from left to right. Even if an alignment is labeled as "Plus/Plus, " the encoded gene may be on the minus strand. When the minus strand of the query sequence is similar to a database sequence, the alignment is reported with either the subject or query sequence in reversed coordinates. In NCBI-BLAST, the database sequences are flipped, but in WU-BLAST, the query coordinates are flipped. Las hebras Plus y Minus

BLAST en el NCBI-BLAST (same strand) NCBI-BLAST (different strand) WU-BLAST (different strand) Las hebras Plus y Minus (2)
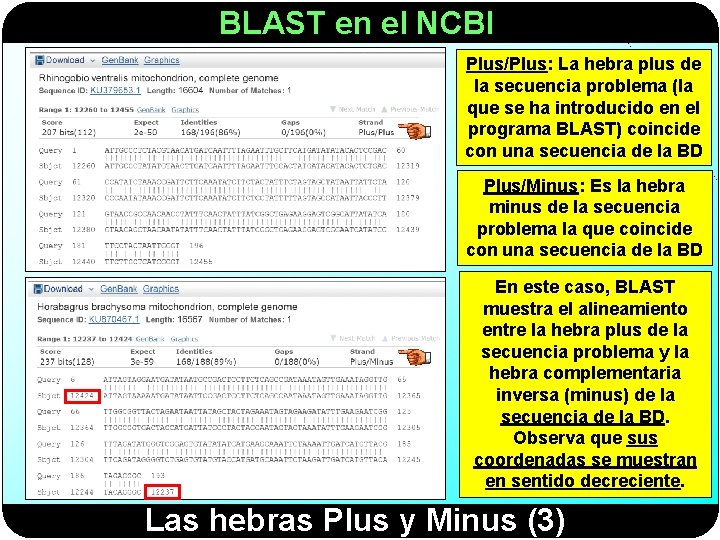
BLAST en el NCBI Plus/Plus: La hebra plus de la secuencia problema (la que se ha introducido en el programa BLAST) coincide con una secuencia de la BD Plus/Minus: Es la hebra minus de la secuencia problema la que coincide con una secuencia de la BD En este caso, BLAST muestra el alineamiento entre la hebra plus de la secuencia problema y la hebra complementaria inversa (minus) de la secuencia de la BD. Observa que sus coordenadas se muestran en sentido decreciente. Las hebras Plus y Minus (3)

BLAST en el NCBI Todos los casos posibles

BLAST en el NCBI
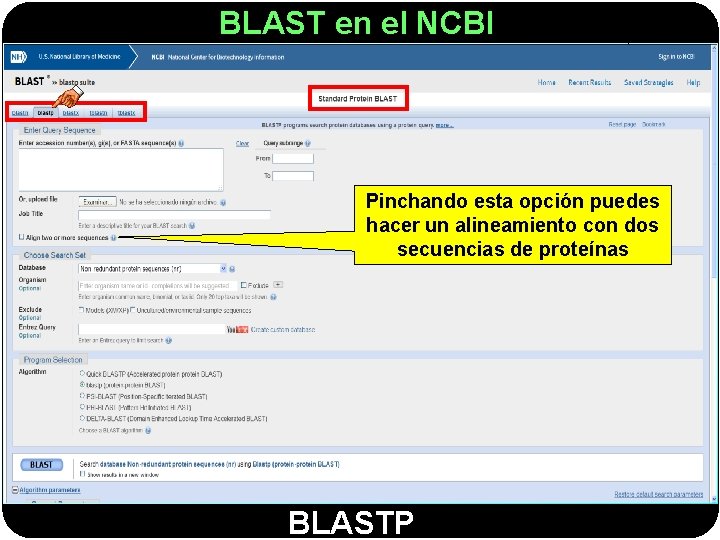
BLAST en el NCBI Pinchando esta opción puedes hacer un alineamiento con dos secuencias de proteínas BLASTP

BLAST en el NCBI Los distintos algoritmos de BLASTP

BLAST en el NCBI DELTA-BLAST

BLAST en el NCBI Se suele utilizar para: 1. - Identificar una proteína (el parecido es del 100%) 2. - Identificar proteínas homólogas 3. - Seleccionar proteínas homólogas de varios organismos para hacer alineamientos múltiples de secuencia o análisis filogenéticos 4. - Identificar regiones comunes en proteínas distintas (dominios locales conservados) Usos de BLASTP
BLAST en el NCBI
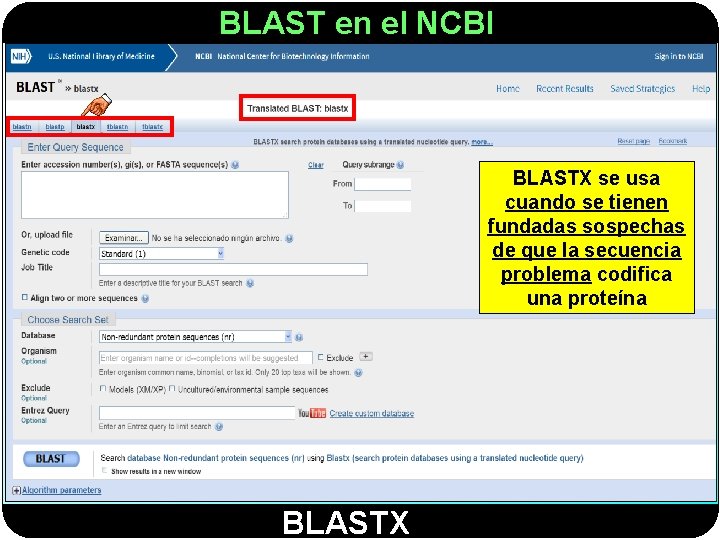
BLAST en el NCBI BLASTX se usa cuando se tienen fundadas sospechas de que la secuencia problema codifica una proteína BLASTX

BLAST en el NCBI BLASTX permite determinar si una secuencia de nucleótidos recién obtenida codifica una proteína Se suele utilizar para: 1. - Localizar genes que codifican proteínas en el ADN genómico 2. - Determinar si un transcrito (en forma de ADNc o EST) corresponde a una proteína conocida 3. - Distinguir las regiones codificantes y no codificantes (5’-UTR y 3’-UTR) de un ARNm Usos de BLASTX

BLAST en el NCBI Avanzan de 3 en 3 Avanzan de 1 en 1 BLASTX Alignments from BLASTX are complicated by both strand reading frame. The query sequence is translated in three frames on both the plus and minus strands. With three nucleotides per codon, the coordinates of the query sequence increase by threes. Minus strand matches invert the query coordinates.
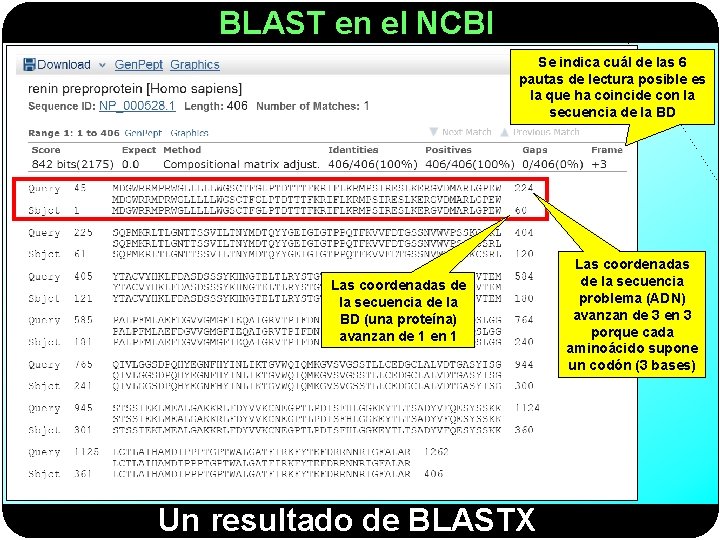
BLAST en el NCBI Se indica cuál de las 6 pautas de lectura posible es la que ha coincide con la secuencia de la BD Las coordenadas de la secuencia de la BD (una proteína) avanzan de 1 en 1 Un resultado de BLASTX Las coordenadas de la secuencia problema (ADN) avanzan de 3 en 3 porque cada aminoácido supone un codón (3 bases)
BLAST en el NCBI
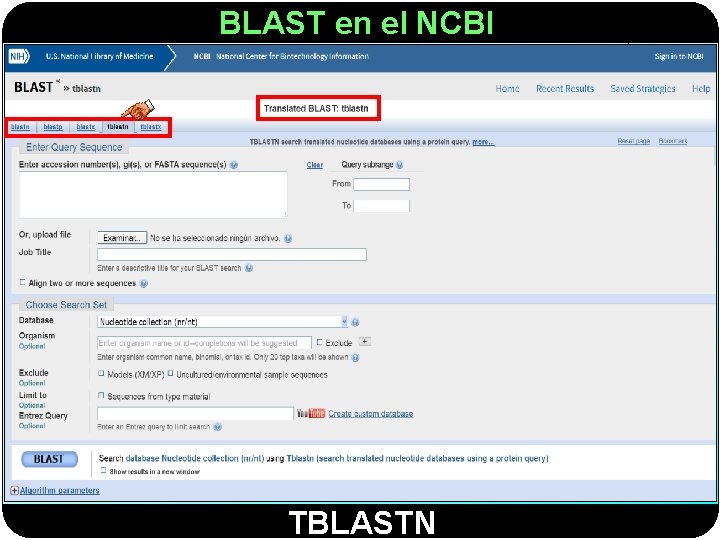
BLAST en el NCBI TBLASTN

BLAST en el NCBI TBLASTN se usa cuando BLASTP no ha encontrado nada porque la secuencia problema aún no aparece en las BD de proteínas Se suele utilizar para: 1. - Localizar una proteína en el ADN genómico 2. - Localizar exones en el ADN genómico 3. - Identificar los transcritos (en forma de ADNc o EST) de organismos poco caracterizados, que puedan corresponder a la proteína problema o a una proteína homóloga Usos de TBLASTN

BLAST en el NCBI TBLASTN
BLAST en el NCBI
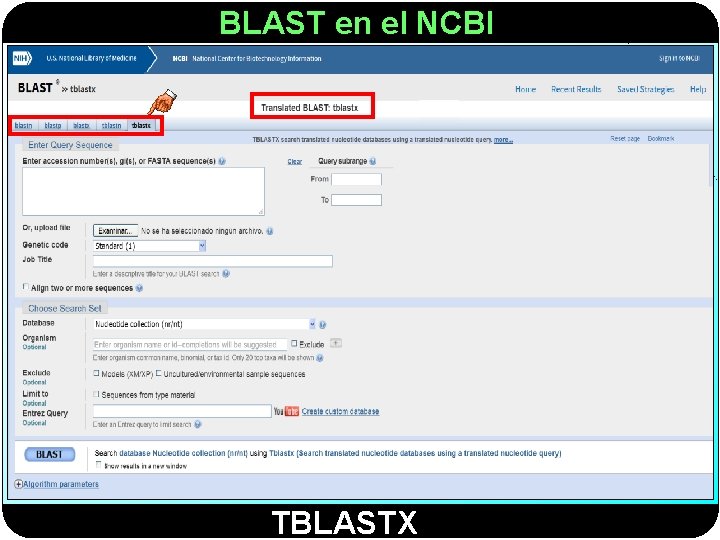
BLAST en el NCBI TBLASTX

BLAST en el NCBI TBLASTX se utiliza para localizar genes difíciles de encontrar mediante métodos convencionales Se suele utilizar para: 1. - Descubrir en el ADN genómico nuevos genes (en la misma especie o en especies distintas) que no han sido encontrados por métodos tradicionales (genes dentro de genes, procesamientos alternativos o genes con bajo nivel de expresión) 2. - Descubrir transcritos (en forma de ADNc o EST) cuyos productos aún no están en las BD de proteínas Usos de TBLASTX

BLAST en el NCBI TBLASTX

BLAST en el NCBI 6 pautas de lectura posibles en cada secuencia
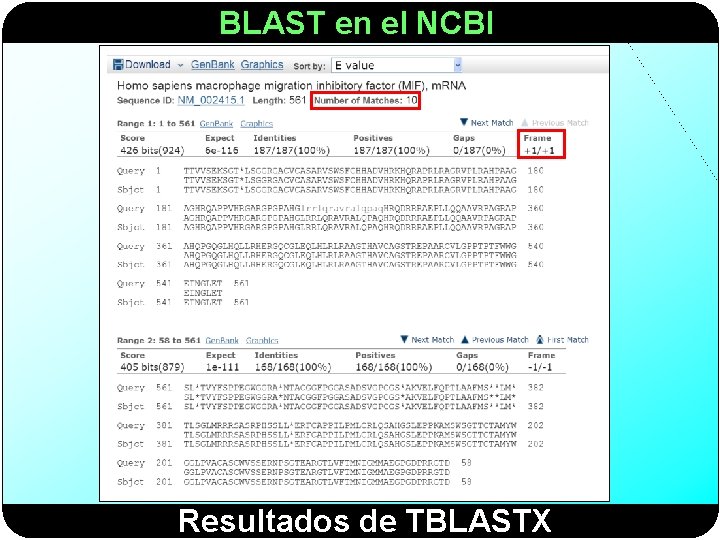
BLAST en el NCBI Resultados de TBLASTX

BLAST en el NCBI Algunas recomendaciones
- Slides: 72