Biophysics of Systems Dieter Braun Systems Biophysics Lecture
Biophysics of Systems Dieter Braun Systems Biophysics Lecture + Seminar Do 14. 15 -17. 30 Uhr Website of Lecture: http: //www. physik. uni-muenchen. de/ lehre/vorlesungen/wise_09_10/ Biophysics_of_Systems/index. html Master Program Biophysics: http: //www. physik. uni-muenchen. de/studium/ studiengaenge/master_physik/ma_phys_bio/curriculum. html

Inhalte : Biophysik der Systeme 1. Einleitung 2. Evolution + Nichtlineare Dynamik 3. Raumzeitliche Strukturbildung 4. Biologische Netzwerke 5. Beispiel: Chemotaxis 6. Genetische Netzwerke 7. Zelluläre Netzwerke / Neuronale Netze 8. Spieltheorie 9. Methoden der Systembiologie 10. Synthetische Biologie

Makrophage jagt E. coli Bakterium
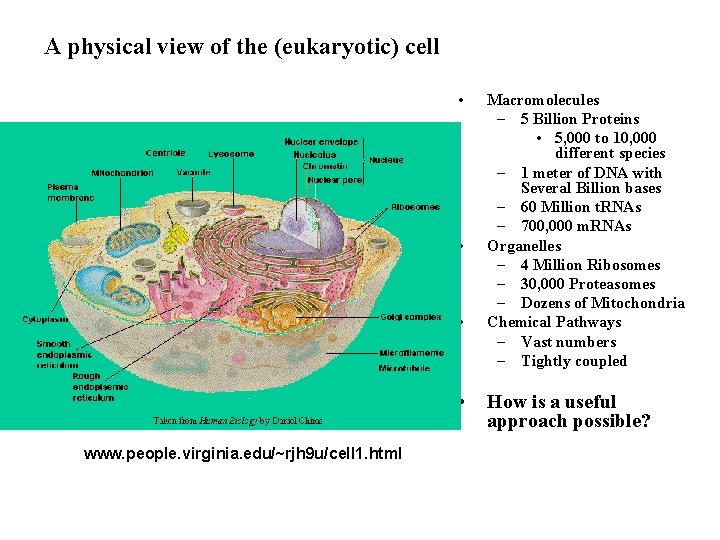
A physical view of the (eukaryotic) cell • • www. people. virginia. edu/~rjh 9 u/cell 1. html Macromolecules – 5 Billion Proteins • 5, 000 to 10, 000 different species – 1 meter of DNA with Several Billion bases – 60 Million t. RNAs – 700, 000 m. RNAs Organelles – 4 Million Ribosomes – 30, 000 Proteasomes – Dozens of Mitochondria Chemical Pathways – Vast numbers – Tightly coupled How is a useful approach possible?
Biosystems: Rückkopplungen
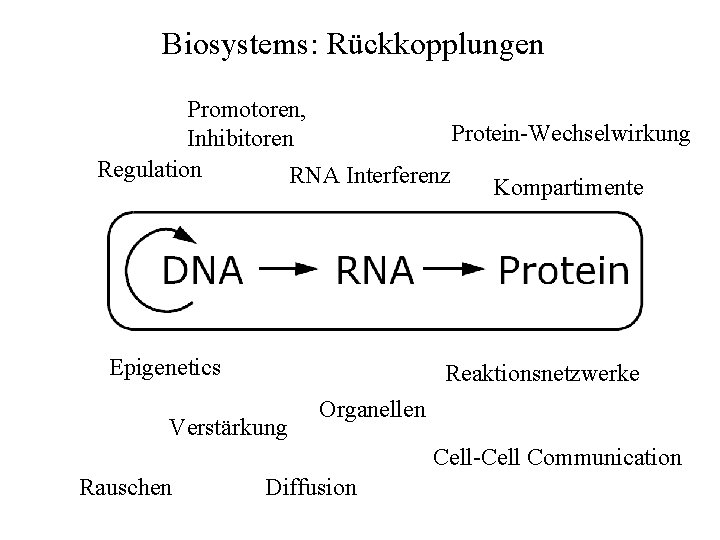
Biosystems: Rückkopplungen Promotoren, Protein-Wechselwirkung Inhibitoren Regulation RNA Interferenz Kompartimente Epigenetics Reaktionsnetzwerke Verstärkung Organellen Cell-Cell Communication Rauschen Diffusion
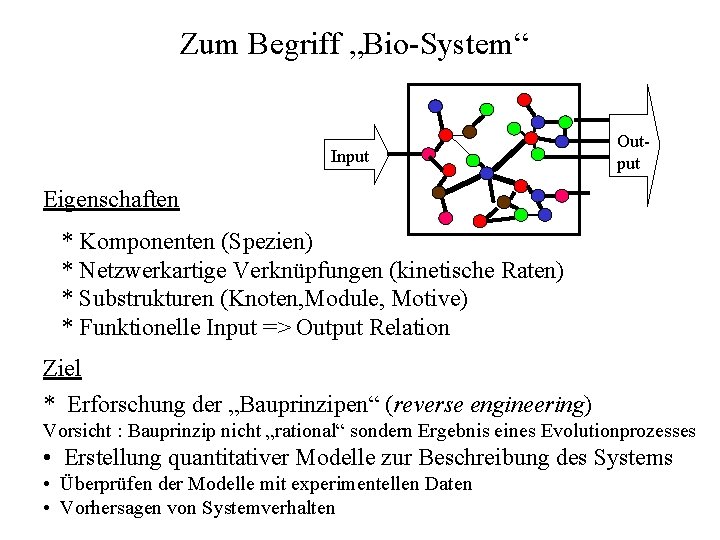
Zum Begriff „Bio-System“ Input Output Eigenschaften * Komponenten (Spezien) * Netzwerkartige Verknüpfungen (kinetische Raten) * Substrukturen (Knoten, Module, Motive) * Funktionelle Input => Output Relation Ziel * Erforschung der „Bauprinzipen“ (reverse engineering) Vorsicht : Bauprinzip nicht „rational“ sondern Ergebnis eines Evolutionprozesses • Erstellung quantitativer Modelle zur Beschreibung des Systems • Überprüfen der Modelle mit experimentellen Daten • Vorhersagen von Systemverhalten

Systems Biology Definition • Systems Biology integrates experimental and modeling approaches to study the structure and dynamical properties of biological systems • It aims at quantitative experimental results and building predictive models and simulations of these systems. • Current primary focus is the cell and its subsystems , but the „systems perspective“ will be extended to tissues, organisms, populations, ecosystems, . .
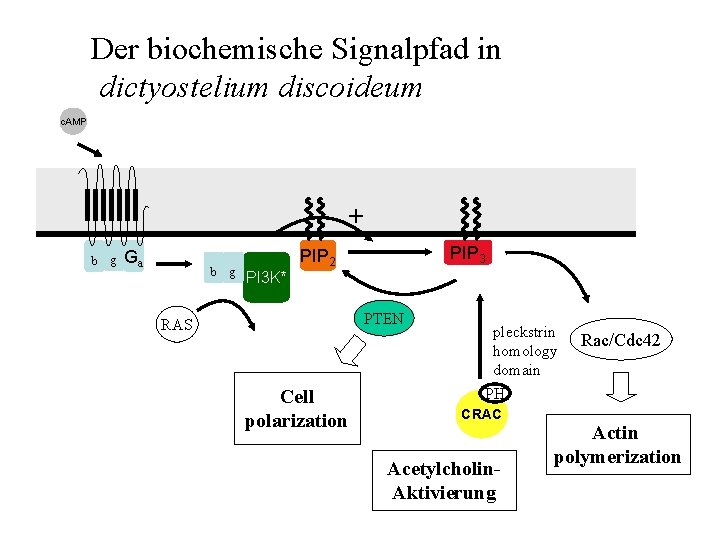
Der biochemische Signalpfad in dictyostelium discoideum c. AMP + b g Ga b g PI 3 K* PIP 3 PIP 2 PTEN RAS Cell polarization pleckstrin homology domain PH CRAC Acetylcholin. Aktivierung Rac/Cdc 42 Actin polymerization
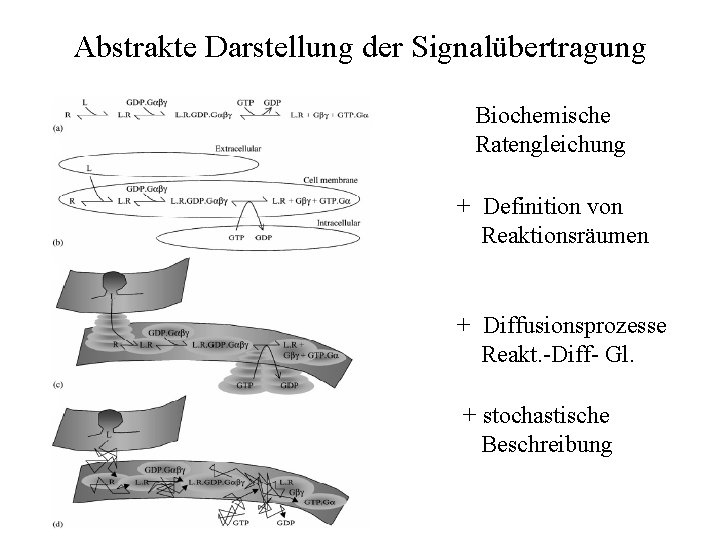
Abstrakte Darstellung der Signalübertragung Biochemische Ratengleichung + Definition von Reaktionsräumen + Diffusionsprozesse Reakt. -Diff- Gl. + stochastische Beschreibung
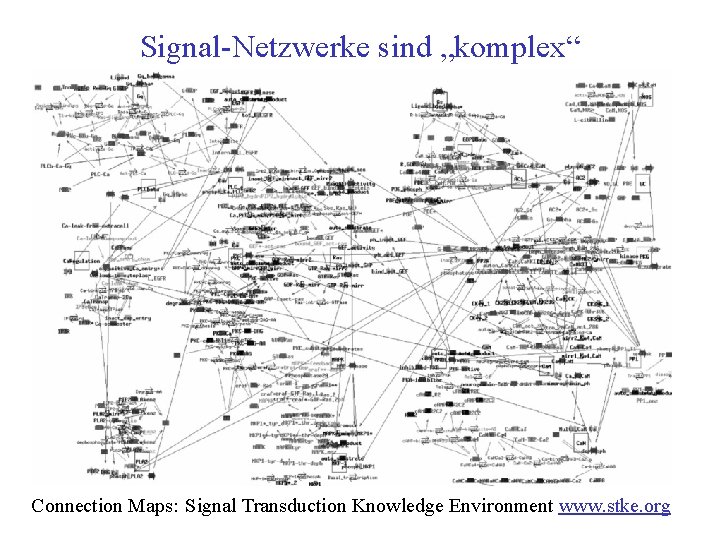
Signal-Netzwerke sind „komplex“ Connection Maps: Signal Transduction Knowledge Environment www. stke. org

Zum Umgang mit Komplexität
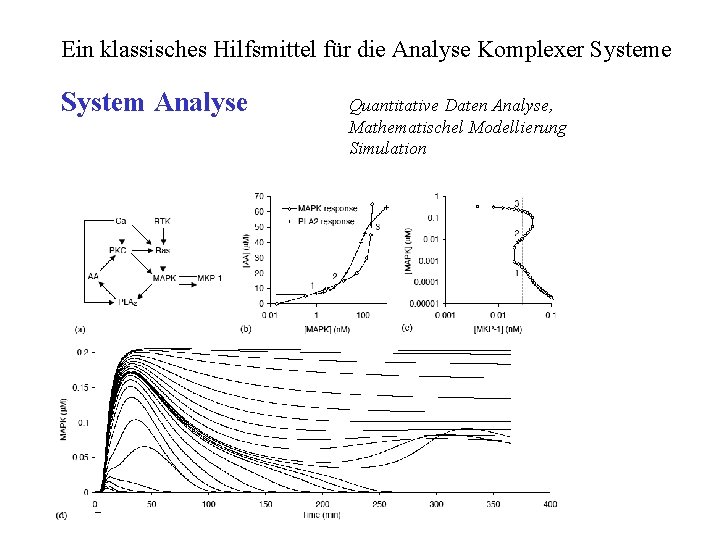
Ein klassisches Hilfsmittel für die Analyse Komplexer Systeme System Analyse Quantitative Daten Analyse, Mathematischel Modellierung Simulation
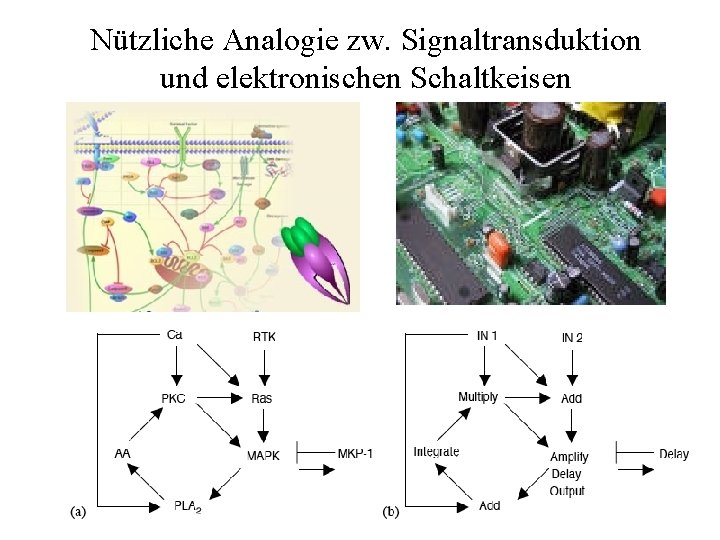
Nützliche Analogie zw. Signaltransduktion und elektronischen Schaltkeisen
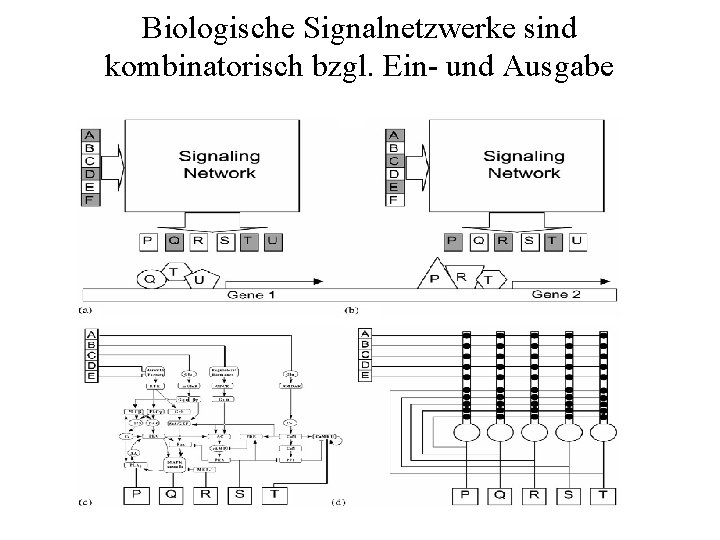
Biologische Signalnetzwerke sind kombinatorisch bzgl. Ein- und Ausgabe
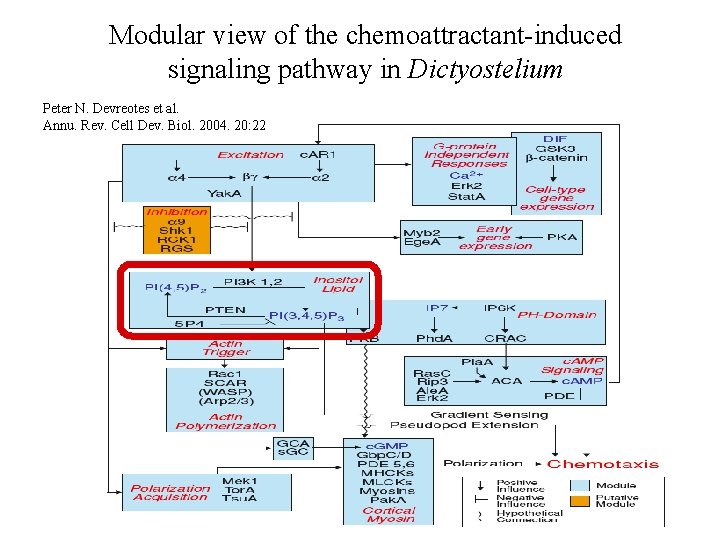
Modular view of the chemoattractant-induced signaling pathway in Dictyostelium Peter N. Devreotes et al. Annu. Rev. Cell Dev. Biol. 2004. 20: 22
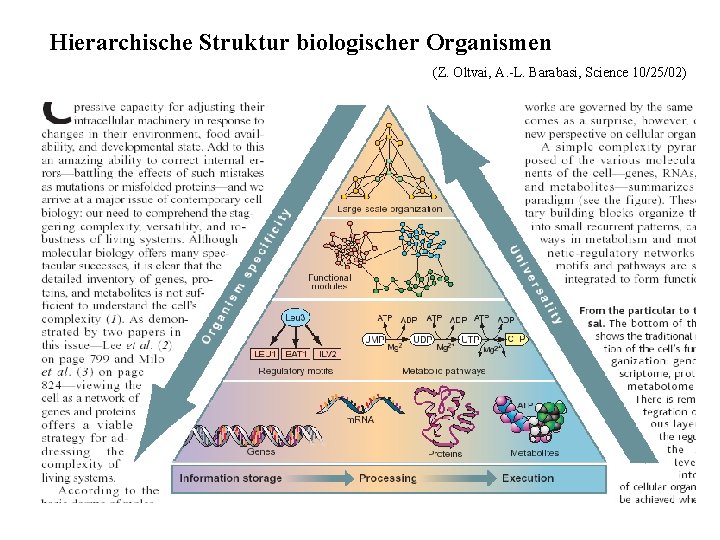
Hierarchische Struktur biologischer Organismen (Z. Oltvai, A. -L. Barabasi, Science 10/25/02)

Modular Biology as advocated in the influential paper (Nature 402, Dec 1999)

Stochastic Genes From Concentrations to Probabilities

Stochastic Genes From Concentrations to Probabilities Inventory of an E-coli: do counting molecules matter? Note the low number of m. RNA !
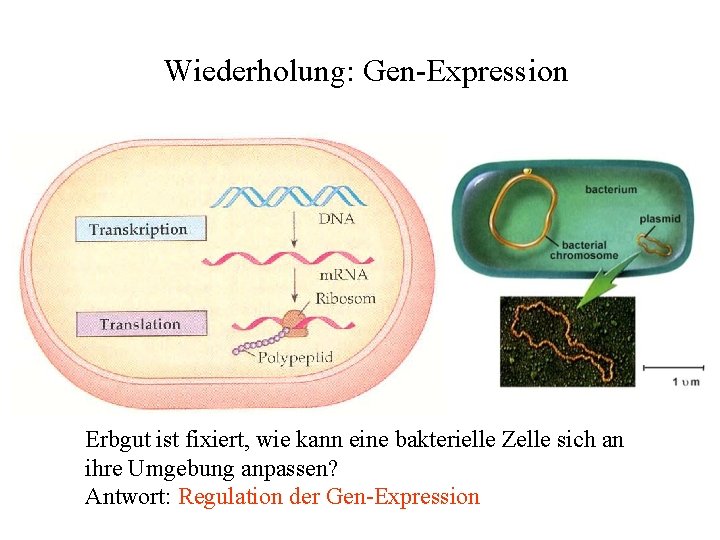
Wiederholung: Gen-Expression Erbgut ist fixiert, wie kann eine bakterielle Zelle sich an ihre Umgebung anpassen? Antwort: Regulation der Gen-Expression
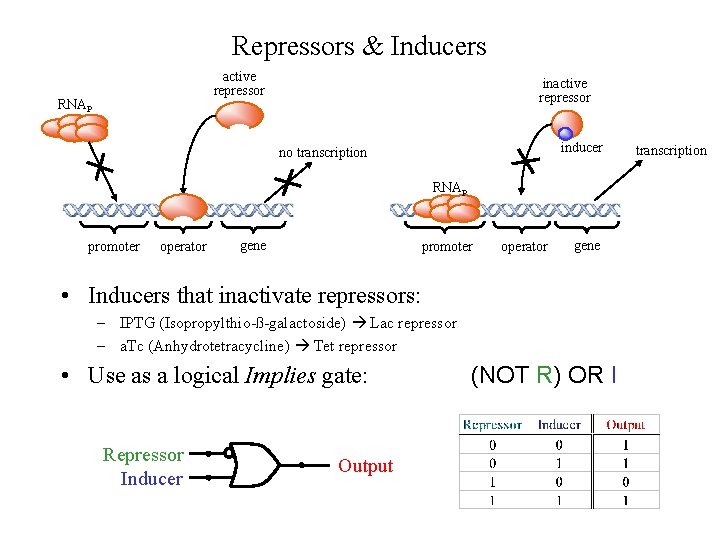
Repressors & Inducers active repressor RNAP inactive repressor inducer no transcription RNAP promoter operator gene • Inducers that inactivate repressors: – IPTG (Isopropylthio-ß-galactoside) Lac repressor – a. Tc (Anhydrotetracycline) Tet repressor • Use as a logical Implies gate: Repressor Inducer Output (NOT R) OR I transcription
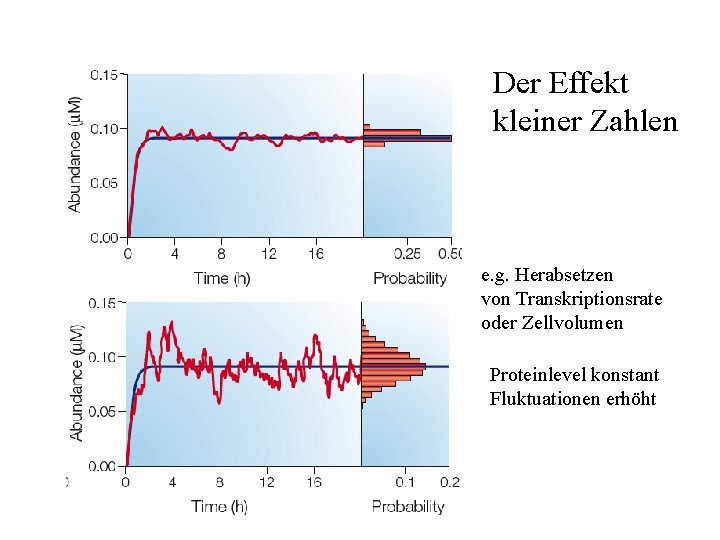
Der Effekt kleiner Zahlen e. g. Herabsetzen von Transkriptionsrate oder Zellvolumen Proteinlevel konstant Fluktuationen erhöht
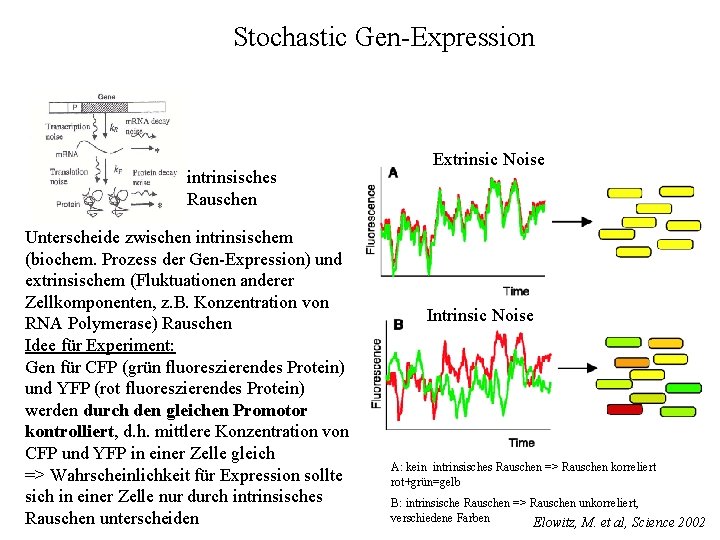
Stochastic Gen-Expression intrinsisches Rauschen Unterscheide zwischen intrinsischem (biochem. Prozess der Gen-Expression) und extrinsischem (Fluktuationen anderer Zellkomponenten, z. B. Konzentration von RNA Polymerase) Rauschen Idee für Experiment: Gen für CFP (grün fluoreszierendes Protein) und YFP (rot fluoreszierendes Protein) werden durch den gleichen Promotor kontrolliert, d. h. mittlere Konzentration von CFP und YFP in einer Zelle gleich => Wahrscheinlichkeit für Expression sollte sich in einer Zelle nur durch intrinsisches Rauschen unterscheiden Extrinsic Noise Intrinsic Noise A: kein intrinsisches Rauschen => Rauschen korreliert rot+grün=gelb B: intrinsische Rauschen => Rauschen unkorreliert, verschiedene Farben Elowitz, M. et al, Science 2002
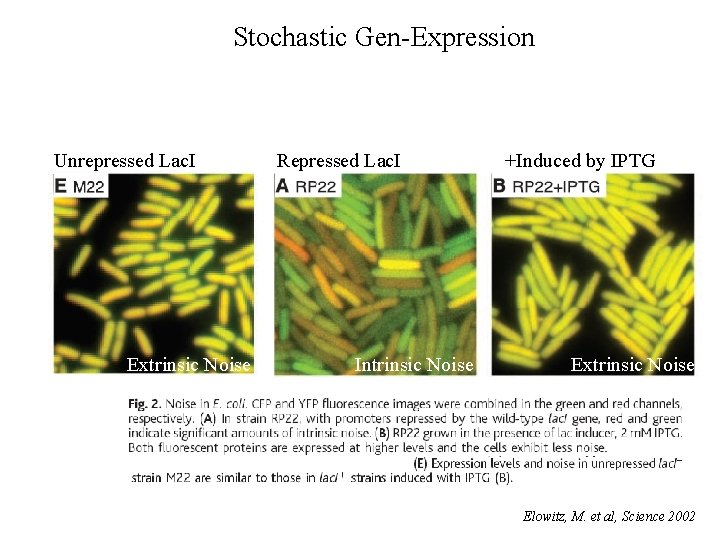
Stochastic Gen-Expression Unrepressed Lac. I Extrinsic Noise Repressed Lac. I Intrinsic Noise +Induced by IPTG Extrinsic Noise Elowitz, M. et al, Science 2002

Science, 307: 1965 (2005)
- Slides: 26