Bioinformatique LIRMM Montpellier Logiciels et serveurs Gnomique comparative

Bio-informatique LIRMM Montpellier Logiciels et serveurs Génomique comparative et fonctionnelle

Equipe bioinformatique du LIRMM • 6 Permanents V. Berry (Md. C, UM 2), L. Bréhelin (CR, CNRS), G. Caraux (Prof Agro Mpl), O. Gascuel (DR CNRS), O. Martin (CR, INRA), E. Rivals (CR, CNRS) • 2 Associés A. Jean-Marie (DR, INRIA), G. Mélançon (Prof, UM 3) • 1 Ingénieur Génopole S. Pinloche, puis F. Le Thiec • 8 Doctorants • 1 Post-doctorant

Equipe bioinformatique du LIRMM • Actions – régionales … Génopole Languedoc-Roussillon … – nationales Animation communauté nationale IMPG Lancement de JOBIM (conf. francophone) Responsable de l’ACI IMPBio – internationales Membre du bureau editorial de Systematic Biology Current Protocols in Bioinformatics Comite de Progr. conférences, revues (ECCB, WABI)

Equipe bioinformatique du LIRMM • Collaborations – régionales MP Lefranc, J. Buard (IGH, Montpellier) N Galtier (GPIA, Montpellier) E. Douzery (ISEM, Montpellier) P. Jarne (CEFE, Montpellier) L. Journot (CCIPE, Montpellier) – nationales… – internationales M. Hendy (Massey Univ. , NZ) G. Weiner (Australian National University, AU) R. Desper (NCBI, USA) F. Major (Univ. de Montreal, CA) S. Rahmann, M. Vingron (Max Planck Institute, GER)

Equipe bioinformatique du LIRMM • Publications 2002 -03 – Discrete Applied Mathematics – Combinatorics, Probability and Computing – Lecture Notes in Computer Science (2 articles) – Journal of Computational Biology (2 articles) – Bioinformatics – Systematic Biology – Proteomics – Molecular Biology and Evolution (3 articles)

Equipe bioinformatique du LIRMM • Valorisation sur le portail web – DTscore recontruction d’arbres de duplication – Fast. ME reconstruction phylogénétique – GAME inférence phylogénétique, estima° de gamma – MSAlign alignement de cartes de minisatellites – STAR recherche de répétitions de motifs – Permut. Matrix visualisation de données d’expression – PHYML reconstruction phylogénétique
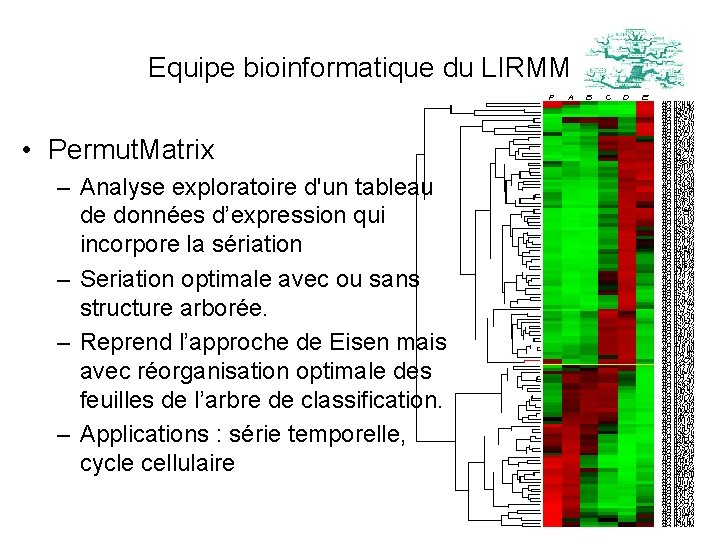
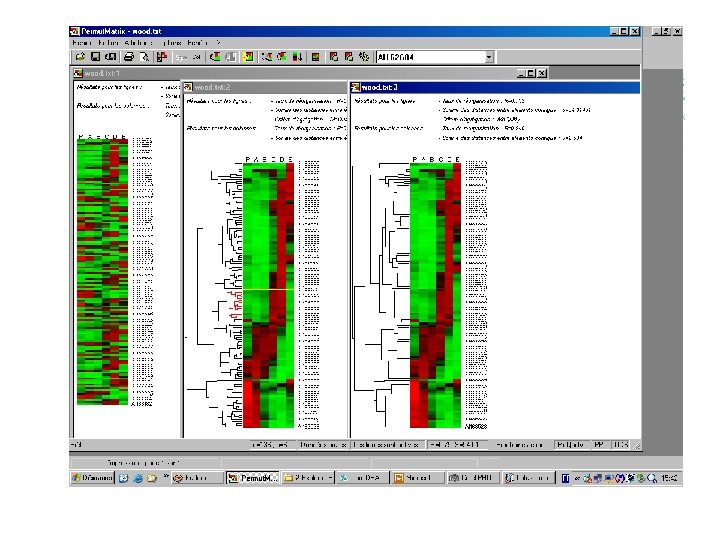
Equipe bioinformatique du LIRMM • Permut. Matrix – Analyse exploratoire d'un tableau de données d’expression qui incorpore la sériation – Seriation optimale avec ou sans structure arborée. – Reprend l’approche de Eisen mais avec réorganisation optimale des feuilles de l’arbre de classification. – Applications : série temporelle, cycle cellulaire
Equipe bioinformatique du LIRMM

Equipe bioinformatique du LIRMM • Permut. Matrix – article soumis à Bioinformatics – implication de S. Pinloche – www. lirmm. fr/~caraux/Permut. Matrix/ – nombreux retours positifs

Equipe bioinformatique du LIRMM • PHYML – Reconstruction phylogénétique avec maximum de vraisemblance (“meilleures méthodes”) – Modèles de substitution varies Nucléotides JC 69, K 2 P, F 81, F 84, HKY, TN 93, GTR Acides aminés Dayhoff, JTT, mt. REV – Aussi précis que fast. DNAml, beaucoup + rapide
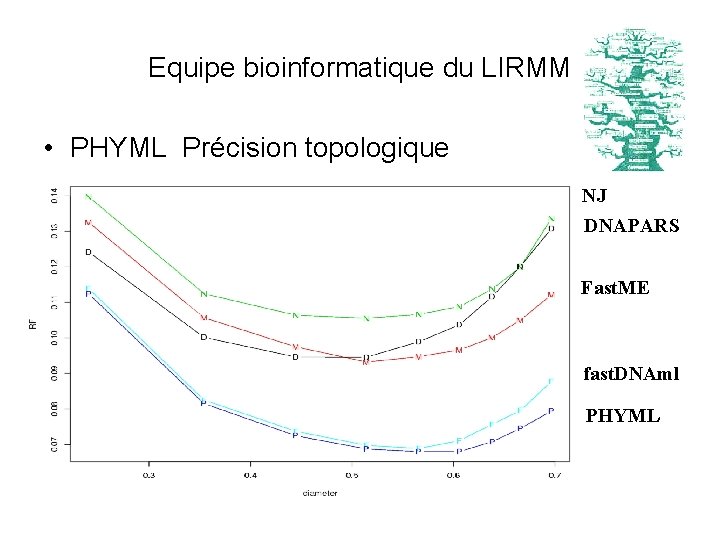
Equipe bioinformatique du LIRMM • PHYML Précision topologique NJ DNAPARS Fast. ME fast. DNAml PHYML
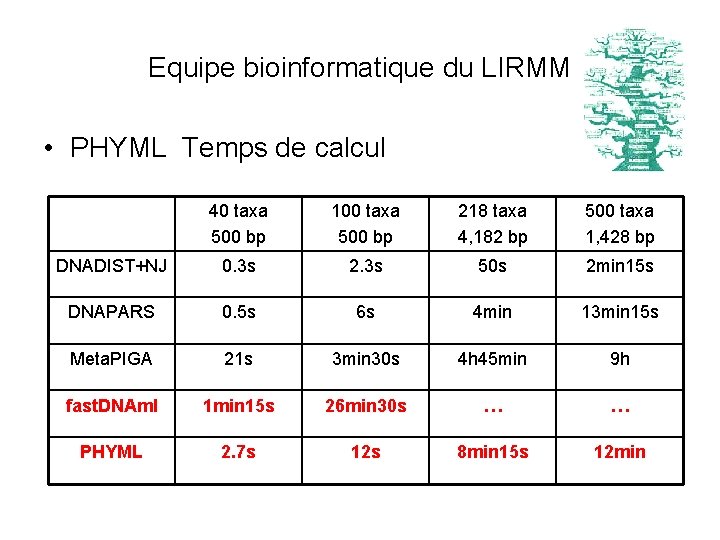
Equipe bioinformatique du LIRMM • PHYML Temps de calcul 40 taxa 500 bp 100 taxa 500 bp 218 taxa 4, 182 bp 500 taxa 1, 428 bp DNADIST+NJ 0. 3 s 2. 3 s 50 s 2 min 15 s DNAPARS 0. 5 s 6 s 4 min 13 min 15 s Meta. PIGA 21 s 3 min 30 s 4 h 45 min 9 h fast. DNAml 1 min 15 s 26 min 30 s … … PHYML 2. 7 s 12 s 8 min 15 s 12 min

Equipe bioinformatique du LIRMM • PHYML – article paru dans Systematic Biology début Oct. – implication de F. Le Thiec – www. lirmm. fr/~guindon/phyml. html – 1100 visites : France, Etats-Unis, Nouvelle-Zélande, Allemagne, Norvège, Canada, Autriche, Royaume. Uni, Suisse, Belgique, Chine…
- Slides: 13