Bioinformatique et Biologie Structurale I Principes et techniques

Bioinformatique et Biologie Structurale I/ – Principes et techniques A/ L’information structurale B/ Les différentes techniques de détermination de structure C/ Les nouveaux challenges de la biologie structurale II/ – Application à l’étude d’enzymes d’intérêt médical A/ Un bref aperçu de ce que l’on appelle « Drug design » B/ Recherche d’inhibiteurs d’aminopeptidases de Streptocoques C/ Relations structure-fonction d’hélicases impliquées dans les cancers
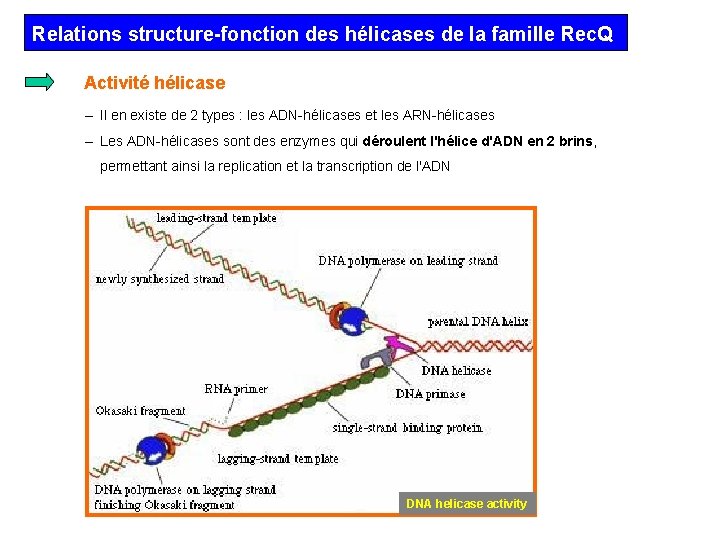
Relations structure-fonction des hélicases de la famille Rec. Q Activité hélicase – Il en existe de 2 types : les ADN-hélicases et les ARN-hélicases – Les ADN-hélicases sont des enzymes qui déroulent l'hélice d'ADN en 2 brins, permettant ainsi la replication et la transcription de l'ADN DNA helicase activity

Relations structure-fonction des hélicases de la famille Rec. Q Fonctionnement d’une ADN-hélicase • Les ADN-hélicases sont des protéines ubiquitaires agissant comme des moteurs moléculaires qui exploitent l’énergie libre fournie par l’hydrolyse de l’ATP pour catalyser la séparation des duplexes d’ADN énergétiquement stables. • On trouve les hélicases chez les procaryotes comme chez les eucaryotes, incluant les virus et les bactériophages. • Ces enzymes rompent les liaisons hydrogène entre les deux brins de l’hélice et se déplacent selon une seule direction sur le brin auquel elles sont liées. • Toutes les hélicases sont aussi des translocases et des ATPases ADN-dépendantes.
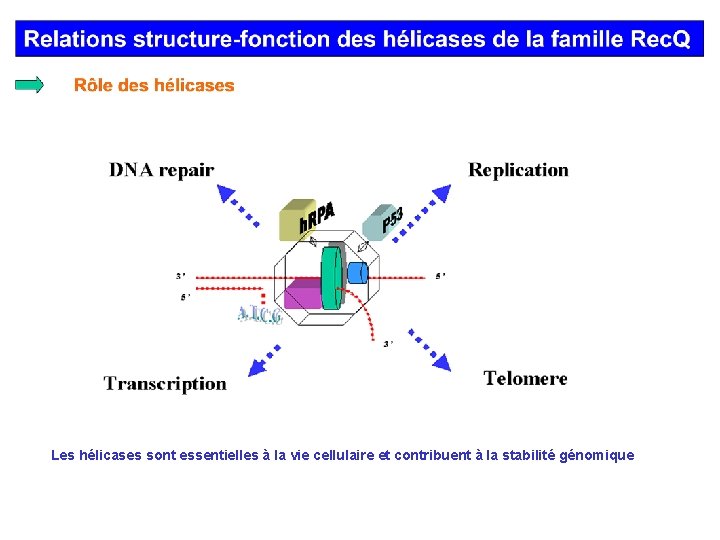
Les hélicases sont essentielles à la vie cellulaire et contribuent à la stabilité génomique

Relations structure-fonction des hélicases de la famille Rec. Q ADN-Hélicases répertoriées • Since the discovery of the first DNA helicase in Escherichia coli in 1976, and the first eukaryotic one in the lily in 1978, a large humain number of these enzymes have been isolated from both prokaryotic and eukaryotic systems, and the number is still growing. • Most contain conserved helicase motifs that act as an engine to power DNA unwinding. • All DNA helicases share some common properties, including nucleic acid binding, NTP binding and hydrolysis, and unwinding of duplex DNA in the 3' to 5' or 5' to 3' direction. E. coli

Relations structure-fonction des hélicases de la famille Rec. Q Family • Les hélicases de la famille Rec. Q sont hautement conservées de la bactérie à l’homme et sont requises dans le maintien de l’intégrité du génome. • Elle sont impliquées dans diverses troubles génétiques humains. • On a répertorié 5 hélicases de la famille Rec. Q chez l’homme : RECQL, WRN, BLM, RECQL 4, et RECQL 5. • Les hélicases de la famille Rec. Q ont été ainsi désignées d’après leur homologies avec l’hélicases de E. coli et partagent des voies de recombinaison similaires. • Toutes hélicases Rec. Q ont des domaines conservés.

Relations structure-fonction des hélicases de la famille Rec. Q Des mutations apparaissant dans WRN et RECQ 4 sont à l’origine, respectivement, des syndromes de Werner et de Rothmund-Thomson. Ces 2 maladies, tout comme le syndrome de Bloom, augmentent la prédisposition individuelle au cancer. Chaque maladie est caractérisée par une instabilité génétique, un cancer, et : Syndrome de Bloom Hair loss/graying - Cataracts Subcutaneous fat loss - Osteoporosis Arteriosclerosis - Diabetes mellitus Syndrome de Werner - vieillissement prématuré Sparse hair - Poikiloderma - Short stature - Cataracts - Skeletal defects Syndrome de Rothmund-Thompson Short stature - Immunodeficiency – Photosensitivity Diabetes mellitus - Male sterility
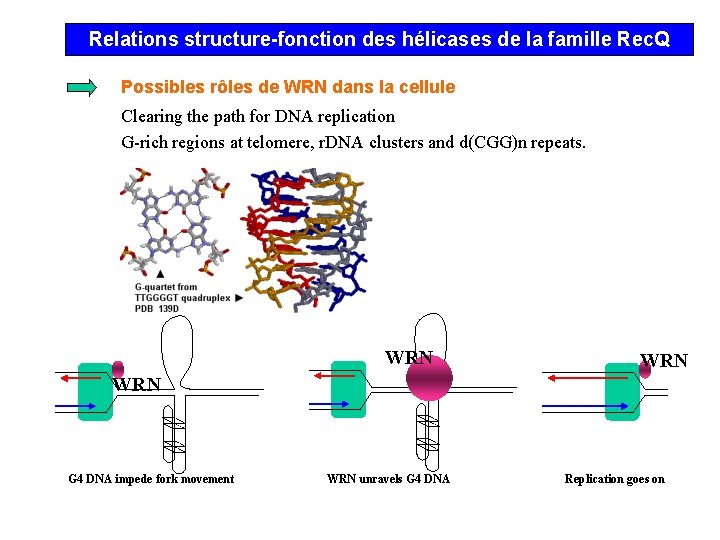
Relations structure-fonction des hélicases de la famille Rec. Q Possibles rôles de WRN dans la cellule Clearing the path for DNA replication G-rich regions at telomere, r. DNA clusters and d(CGG)n repeats. WRN WRN G 4 DNA impede fork movement WRN unravels G 4 DNA Replication goes on
Relations structure-fonction des hélicases de la famille Rec. Q La protéine du Syndrome de Werner impliquée dans le métabolisme du télomère
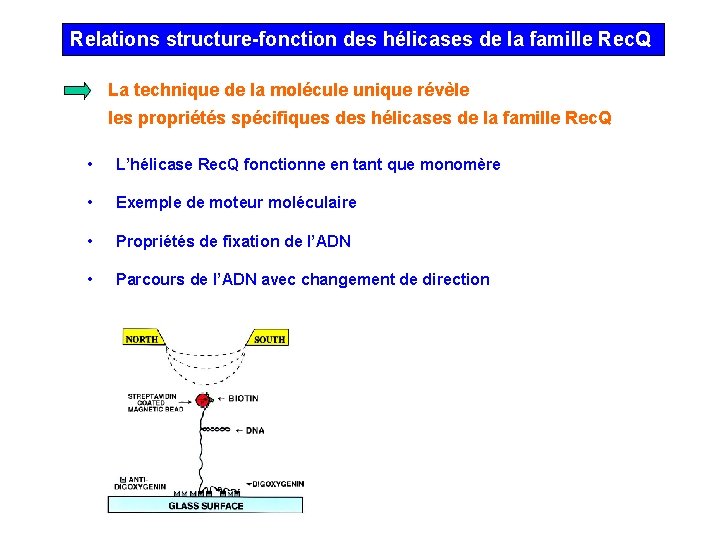
Relations structure-fonction des hélicases de la famille Rec. Q La technique de la molécule unique révèle les propriétés spécifiques des hélicases de la famille Rec. Q • L’hélicase Rec. Q fonctionne en tant que monomère • Exemple de moteur moléculaire • Propriétés de fixation de l’ADN • Parcours de l’ADN avec changement de direction

Relations structure-fonction des hélicases de la famille Rec. Q Vue d’ensemble • Un thématique de recherche axé sur l’étude des relations structure-fonction d’enzymes impliquées dans la régulation du génome et certains cancers • Des expertises complémentaires Biologie Moléculaire Biochimie Enzymologie Bioinformatique Radiocristallographie Physique - Molécule unique
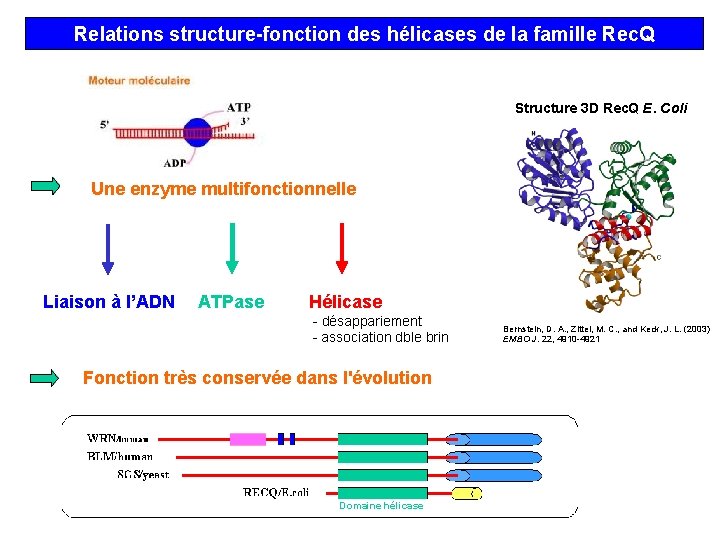
Relations structure-fonction des hélicases de la famille Rec. Q Structure 3 D Rec. Q E. Coli Une enzyme multifonctionnelle Liaison à l’ADN ATPase Hélicase - désappariement - association dble brin Fonction très conservée dans l'évolution Domaine hélicase Bernstein, D. A. , Zittel, M. C. , and Keck, J. L. (2003) EMBO J. 22, 4910 -4921
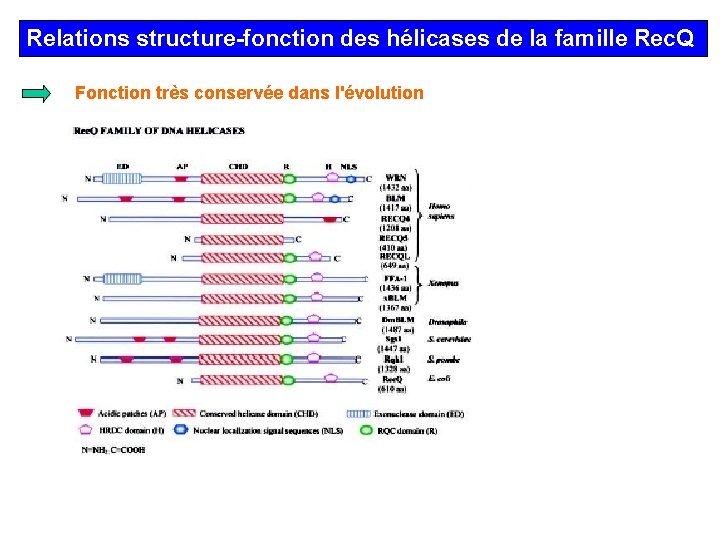
Relations structure-fonction des hélicases de la famille Rec. Q Fonction très conservée dans l'évolution
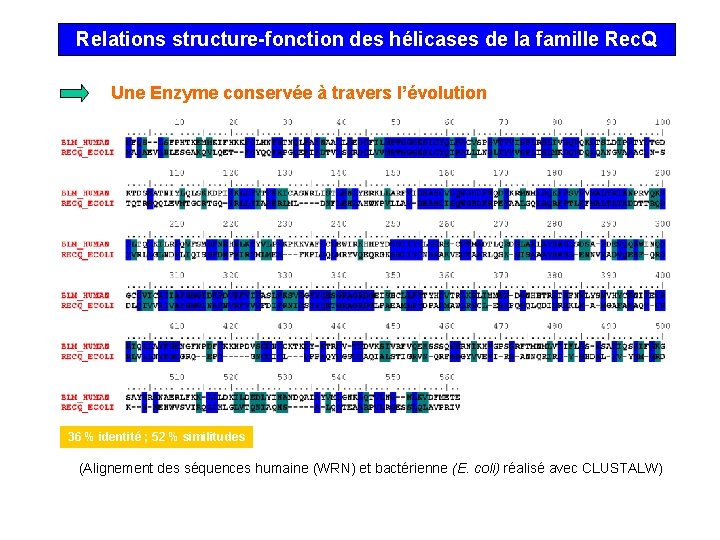
Relations structure-fonction des hélicases de la famille Rec. Q Une Enzyme conservée à travers l’évolution 36 % identité ; 52 % similitudes (Alignement des séquences humaine (WRN) et bactérienne (E. coli) réalisé avec CLUSTALW)
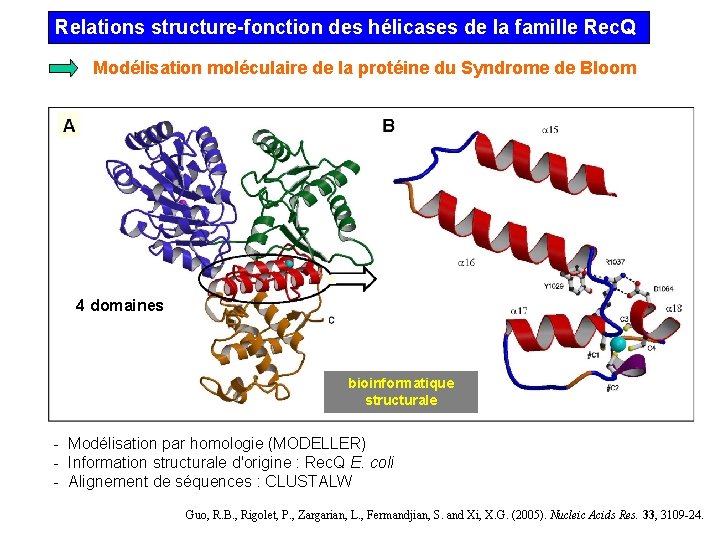
Relations structure-fonction des hélicases de la famille Rec. Q Modélisation moléculaire de la protéine du Syndrome de Bloom 4 domaines bioinformatique structurale - Modélisation par homologie (MODELLER) - Information structurale d'origine : Rec. Q E. coli - Alignement de séquences : CLUSTALW Guo, R. B. , Rigolet, P. , Zargarian, L. , Fermandjian, S. and Xi, X. G. (2005). Nucleic Acids Res. 33, 3109 -24.
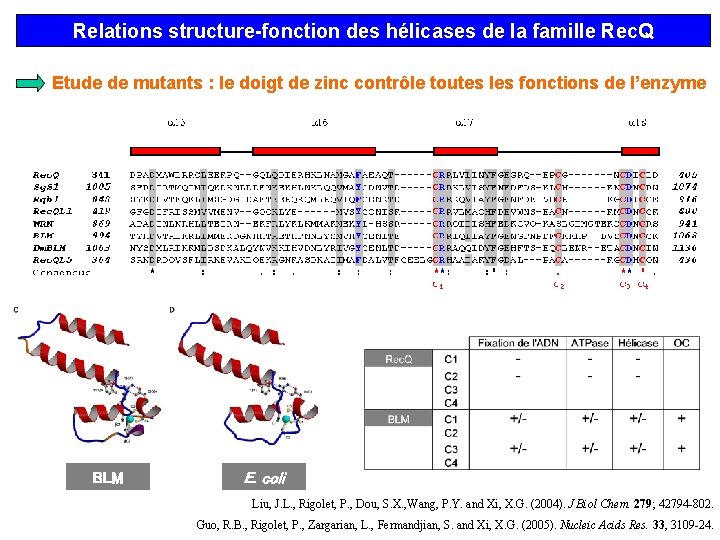
Relations structure-fonction des hélicases de la famille Rec. Q Etude de mutants : le doigt de zinc contrôle toutes les fonctions de l’enzyme BLM E. coli Liu, J. L. , Rigolet, P. , Dou, S. X. , Wang, P. Y. and Xi, X. G. (2004). J Biol Chem. 279; 42794 -802. Guo, R. B. , Rigolet, P. , Zargarian, L. , Fermandjian, S. and Xi, X. G. (2005). Nucleic Acids Res. 33, 3109 -24.
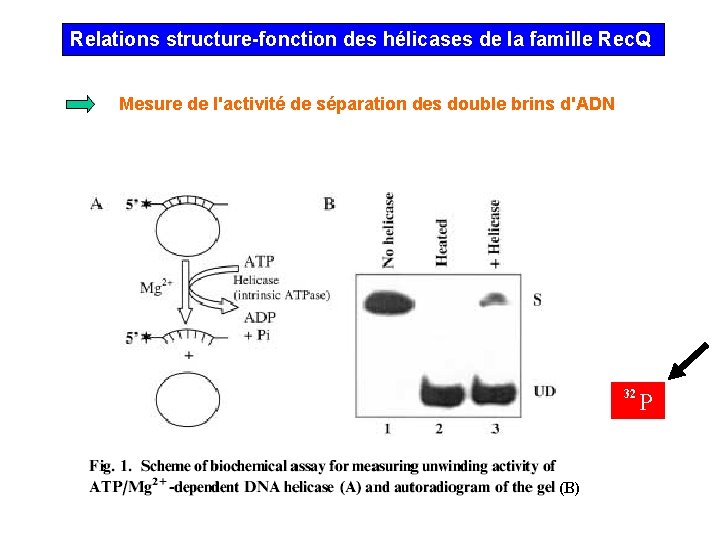
Relations structure-fonction des hélicases de la famille Rec. Q Mesure de l'activité de séparation des double brins d'ADN 32 (B) P
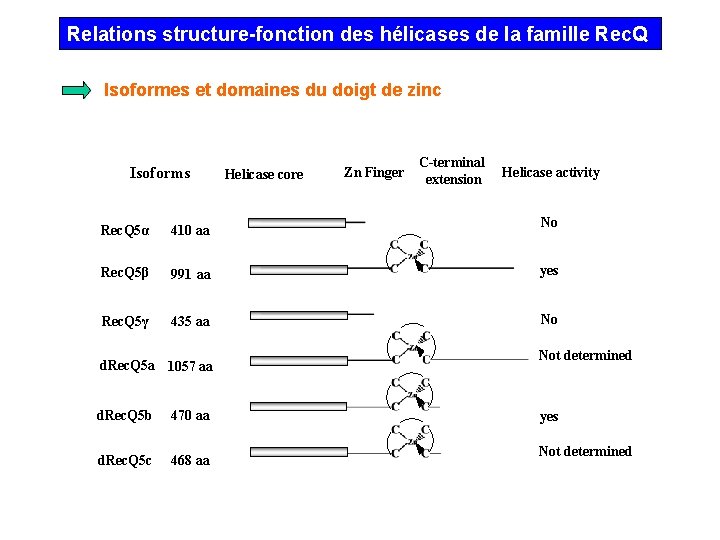
Relations structure-fonction des hélicases de la famille Rec. Q Isoformes et domaines du doigt de zinc Isoforms Helicase core Zn Finger C-terminal extension Helicase activity No Rec. Q 5α 410 aa Rec. Q 5β 991 aa yes Rec. Q 5γ 435 aa No d. Rec. Q 5 a 1057 aa d. Rec. Q 5 b 470 aa d. Rec. Q 5 c 468 aa Not determined yes Not determined
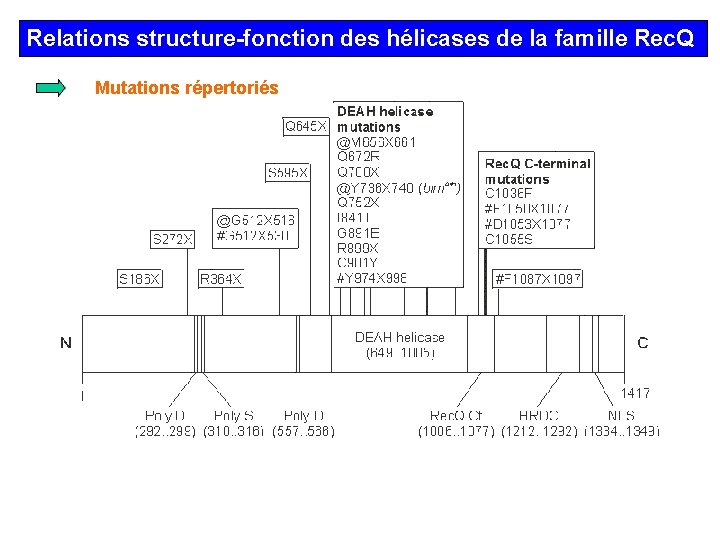
Relations structure-fonction des hélicases de la famille Rec. Q Mutations répertoriés
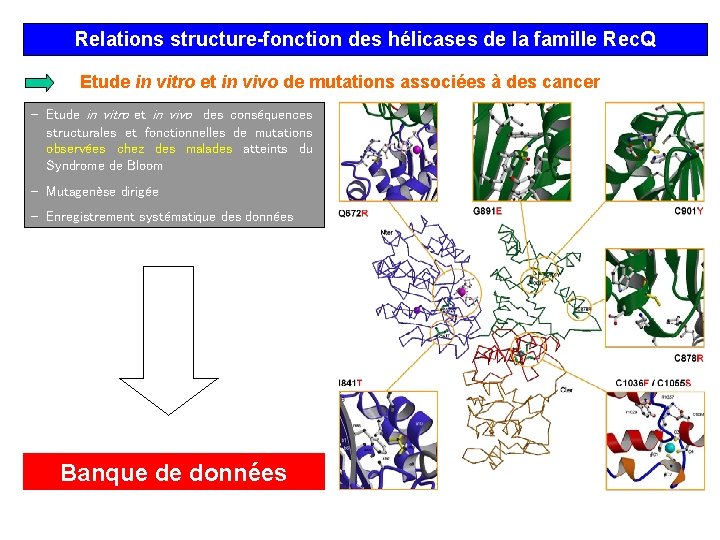
Relations structure-fonction des hélicases de la famille Rec. Q Etude in vitro et in vivo de mutations associées à des cancer - Etude in vitro et in vivo des conséquences structurales et fonctionnelles de mutations observées chez des malades atteints du Syndrome de Bloom - Mutagenèse dirigée - Enregistrement systématique des données Banque de données

Relations structure-fonction des hélicases de la famille de Rec. Q Etude structurale des hélicases BLM, WRN et RECQL 5 Bases moléculaires du fonctionnement de l’enzyme sites de fixation à l’ADN domaines impliqués modélisation des mouvements du moteur moléculaire Enzymes seules complexées à l’ADN Essais de différents ligands de petite taille (inférieure à 20 pdb) simple brin double brin hétéroduplex Nouveau protocole de purification construction sans HIS-Tag Nouvelle technique de cristallisation : microfluidique méthode semi automatique économie de matériel biologique très grand nombre d’essais

Relations structure-fonction des hélicases de la famille Rec. Q Autres projets • Relations avec le télomère • S 3 D enzyme complexé à un motif du télomère • Spécificité vis-à-vis de certains substrats • Effet des métaux autre que zinc • Etude de RIG I, un autre membre la famille Rec. Q [leucémie aiguë]

Relations structure-fonction des hélicases de la famille Rec. Q Cancer et vieillissement prématuré Xu Guang Xi [CR 1] Pascal Rigolet [MCF] Sophia Guo [Doctorante] Collaborations - O. MAUFFRET et S. FERMANDJIAN Structure des Acides Nucléiques et Peptides (Institut G. ROUSSY) Etude en solution du doigt de zinc de BLM en complexe avec l'ADN - V. CROQUETTE et D. BENSIMON Laboratoire de physique statistique – département de biologie (ENS PARIS) Etude des propriétés de Rec. Q par la technique de molécule unique - Thierry BIZEBARD LBPC – Paris - Chen YONG Laboratoire de microfluidique – département de chimie (ENS PARIS)

COLLABORATIONS et FINANCEMENT VA. Bohr NIH USA F. Müller Roche Suisse M. Amor-Gueret Institut Curie Orsay V. Croquette D. Bension Paris Programme PCV CNRS JC. Brochon E. deprez Fluorescence G. Zocchi California USA R. Pansu ENS M. Le Bret Dynamique P. Tauc Imagerie IFR d’Alembert Biologie-Physique-Chimie Z. Chen Shanghai Chine Ligue contre le cancer
- Slides: 24