BASES MOLECULARES DE LA HERENCIA EQUIPO II Gastelum

BASES MOLECULARES DE LA HERENCIA EQUIPO II Gastelum Rosas Emmanuel Ramón Gutiérrez Gil Mario Humberto Azuela Rascon Jesús Alberto

GENOMA ADN Localizacion Funcion

GEN UNIDAD de información genética, secuencia de nucleótidos Expresión Genética Es la lectura de la información en forma de genes Comprende dos etapas: -Transcripción -Traducción
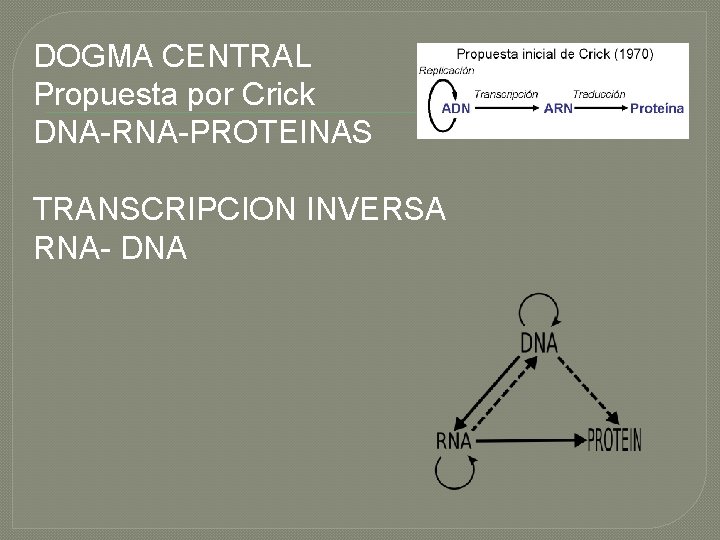
DOGMA CENTRAL Propuesta por Crick DNA-RNA-PROTEINAS TRANSCRIPCION INVERSA RNA- DNA

�EXON �INTRON RNA premensajero RNA mensajero

ACIDOS NUCLEICOS DNA Y RNA Cadenas de nucleótidos unidos por enlaces fosfodiester Nucleótido: Base nitrogenada, Azúcar y un grupo fosfato Base nitrogenada: Purina (AG) o pirimidina (CTU ) Nucleósido: Base nitrogenada, pentosa
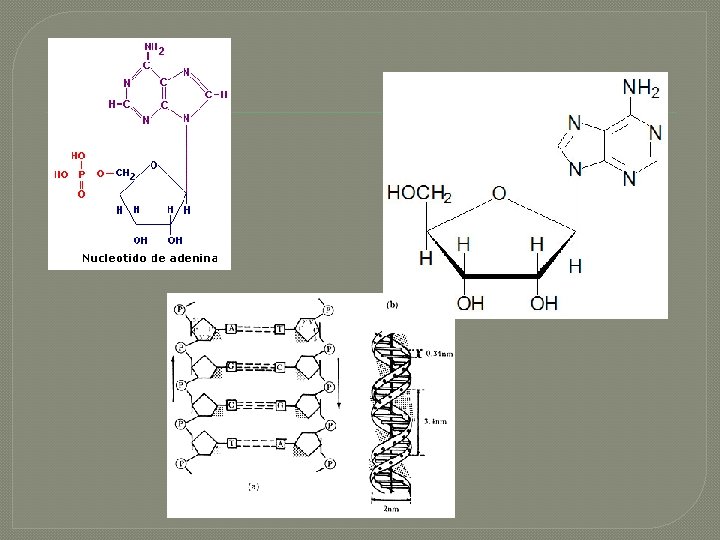

ESTRUCTURA DEL DNA Helicoidal Antiparalera A=T, G=C Bases unidas por puentes hidrogeno -Polinucleotidos -Experimentos de Chargaff (T=A, G=C) -Fotografias de rayos X. 34 nm, 3. 4 nm y 2 nm

SUPERENROLLAMIENTO DEL DNA Giros adicionales en el DNA Topoisomorasas Negativo Positivo

GENOMA HUMANO � NUCLEAR: 99. 9995% 24 moléculas lineales de DNA en doble cadena(22 -x-y) de 50 mb hasta 363 mb cada una contenida en un cromosoma diferente. GC= 42% de las bases Hay cromosomas ricos en genes como el 19 y el 22, o pobres como el 4 y el 18. 3, 300 mb-80 -100 mb tienen una función codificante para polipéptidos

SEUDOGENES Secuencias similares a genes conocidos que no resultan funcionales DNA REPETITIVO NO CODIFICANTE TADEM: Bloques de DNA Satélite: 10 -15% genoma Minisatélite: Microsatélite DISPERSO: Disperso en el genoma Elementos nucleares interespaciado cortos Unidad de repetición de 300 pb, existen 1 millon de copias (7%) Elementos nucleares interespaciados largos 5 -12% del genoma

GENOMA MITOCONDRIAL DNA circular CG=44% Compacto=93% Modelo endosimbiotico Procariota- procariota
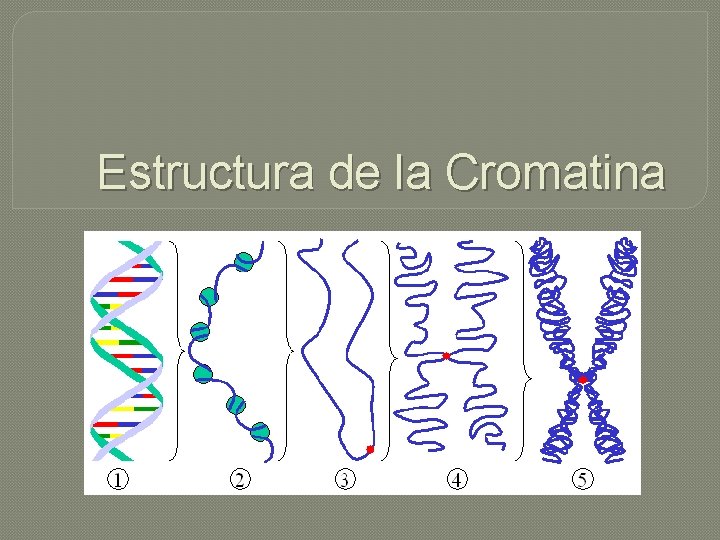
Estructura de la Cromatina

Cromatina – Conceptos Generales �DNA 25 % �RNA 10% �Histonas 25% �Proteínas no Hitonicas 40%

�Histonas: Son los elementos estructurales primarios que ayudan a enrollar y doblar el DNA (H 1, H 2 A, H 2 B, H 3, H 4) �Proteínas no Histonicas: Incluyen los procesos enzimáticos que replican, transcriben y reparan DNA.
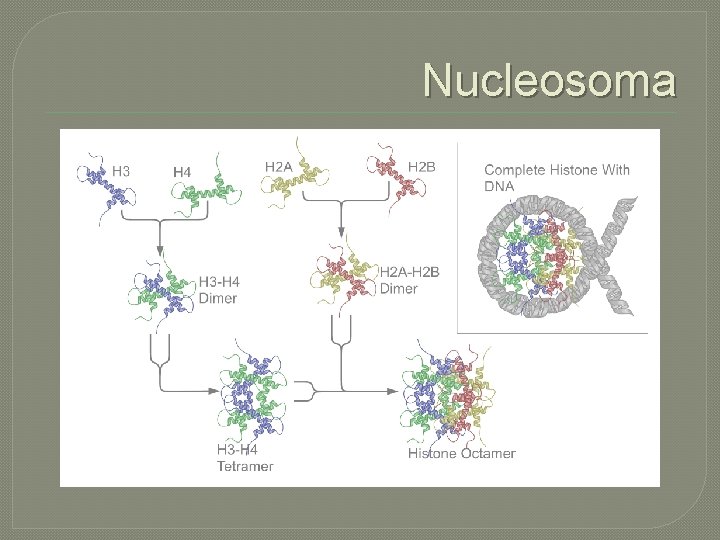
Nucleosoma
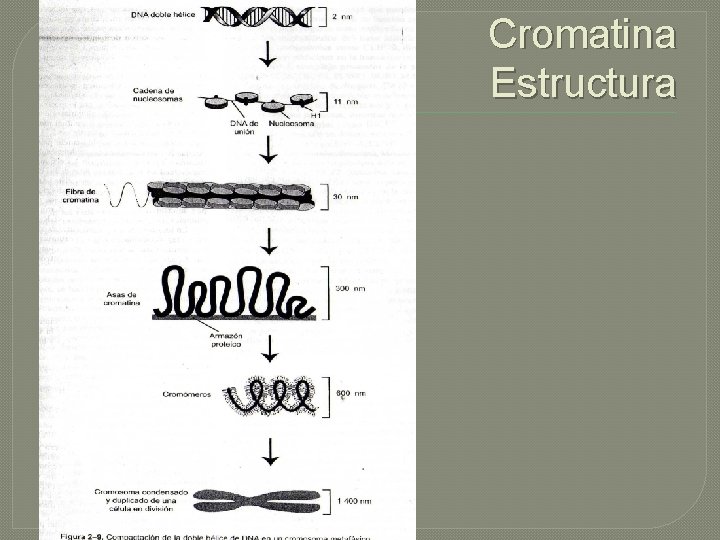
Cromatina Estructura

Cromatina �Eucromatina �Heterocromatina -Constitutiva -Facultativa

Centromero �Interaccion entre cromatina y citoesqueleto durante la division celular �Vinculacion de la cromatides hermanas hasta su migracion en la anafase �Movimiento de los cromosomas durante la anafase
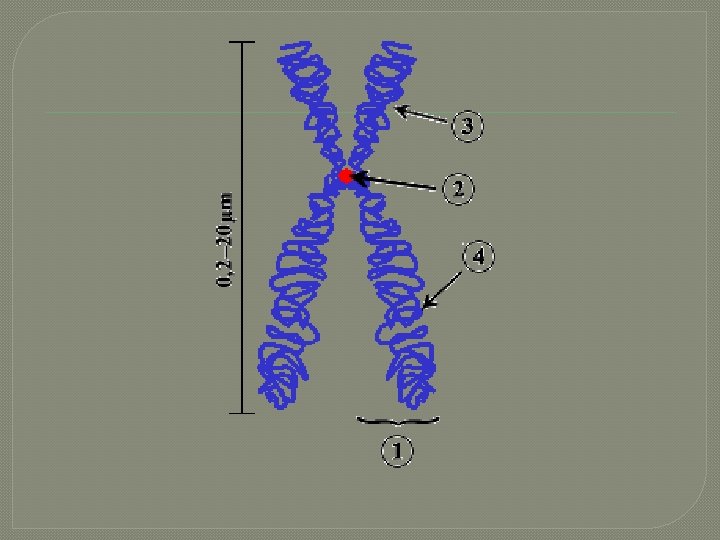
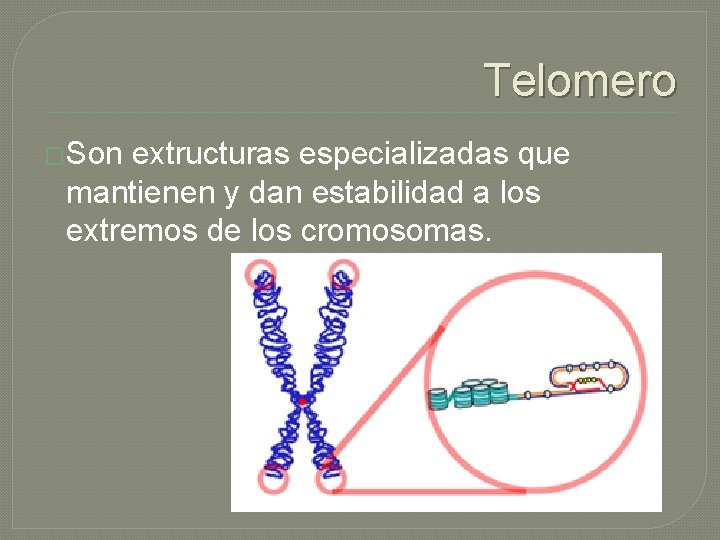
Telomero �Son extructuras especializadas que mantienen y dan estabilidad a los extremos de los cromosomas.

Replicacion �La molécula de DNA debe duplicarse para que al dividirse la célula cada descendiente reciba la misma informacion genética. Replicación

Otras proteínas �PCNA Polimerasas δ y ε �RNAasa H 1 y FEN 1 �DNA Ligasas �DNA Acción coordinada

Antígeno nuclear de proliferación celular (PCNA) �Sliding clamp o balero replicativo. �Anillo que encierra el DNA. �Factor de progresividad para la polimerasa δ. Interviene con Nucleasas FEN 1, Rad 27, MFI DNA ligasa I A L Proteína p 21 N E L A P 53 A TR L N E E D C CDK N R A Ó O I N T C D C A L XPG IN FA E D D R DNA 5 – Citosina metiltransferasa COO ICACIÓN L MLH 1 P E R MSH 2 Ciclina D

DNA Polimerasas δ y ε �DNA Ligasa Inhibe δ y estimula ε. �p 125 le confiere actividad polimerasa y exonucleasa 3’ 5’. p 125 p 50
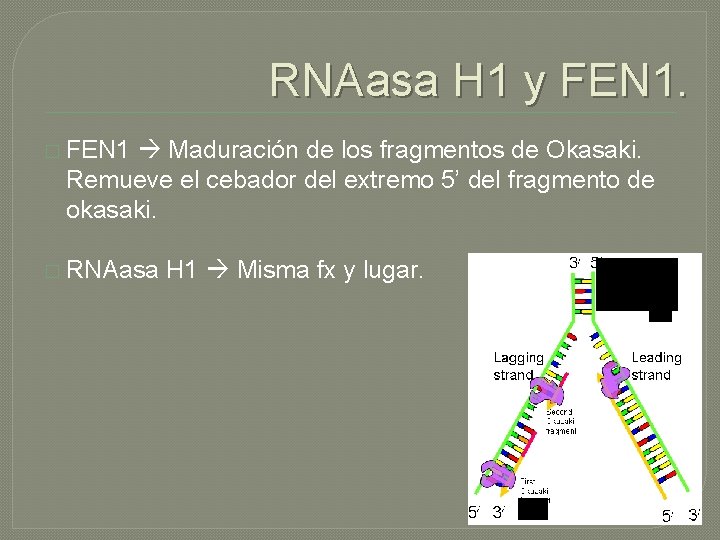
RNAasa H 1 y FEN 1. � FEN 1 Maduración de los fragmentos de Okasaki. Remueve el cebador del extremo 5’ del fragmento de okasaki. � RNAasa H 1 Misma fx y lugar.
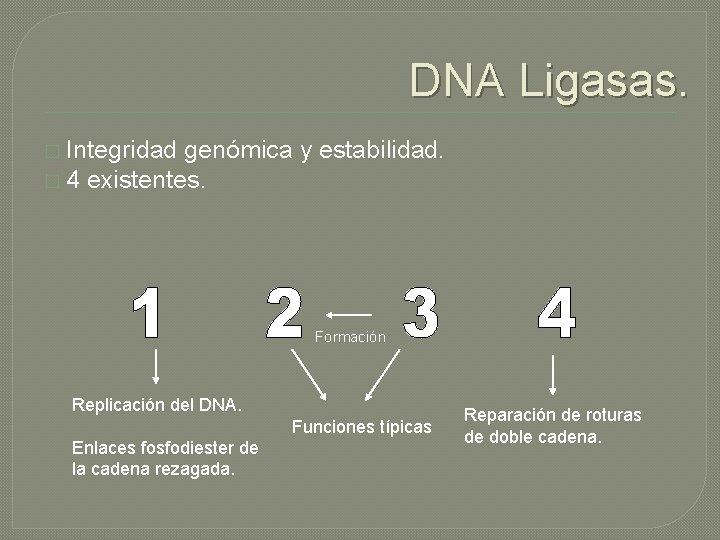
DNA Ligasas. � Integridad genómica y estabilidad. � 4 existentes. Formación Replicación del DNA. Funciones típicas Enlaces fosfodiester de la cadena rezagada. Reparación de roturas de doble cadena.
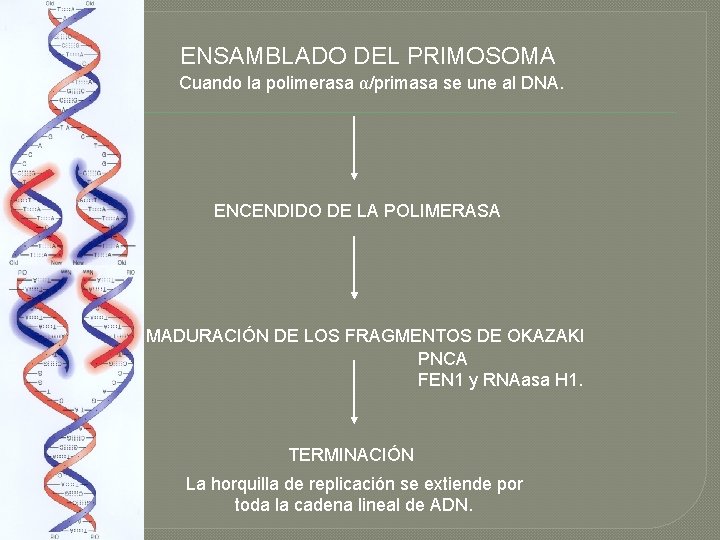
ENSAMBLADO DEL PRIMOSOMA Cuando la polimerasa α/primasa se une al DNA. ENCENDIDO DE LA POLIMERASA MADURACIÓN DE LOS FRAGMENTOS DE OKAZAKI PNCA FEN 1 y RNAasa H 1. TERMINACIÓN La horquilla de replicación se extiende por toda la cadena lineal de ADN.

Encendido de la polimerasa � 1) Se genera un corto de 30 nt. � 2) RFC 3’ � 3) Anclaje del PCNA � 4) Subsiguiente vinculación con la polimerasa δ.
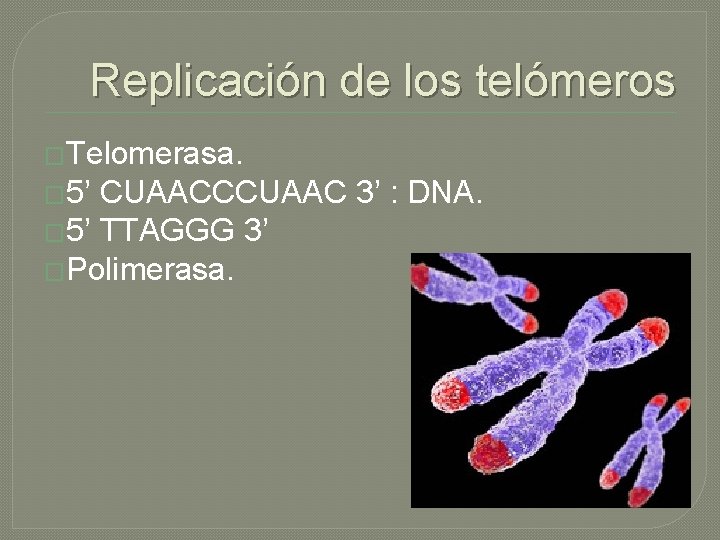
Replicación de los telómeros �Telomerasa. � 5’ CUAACCCUAAC 3’ : DNA. � 5’ TTAGGG 3’ �Polimerasa.

MUTACIÓNES

Mutaciones �Cambio en la secuencia de nucleótidos. � 2 mecanismos: Alteración química de las bases y pérdida o adición de nucleótidos. DIRECTA celular Membrana Físicos AGENTES Químicos Biológicos Agrupación génica INDIRECTA Sistemas enzimáticos SISTEMAS DE TIPOS DE MUTACIÓN PROTECCIÓN

Mecanismos de reparación �Reparación directa �Reparación por escisión de bases. �Reparación por escisión de nucleótidos. �Reparación posreplicativa. �Reparación de bases mal apareadas. Todo modelo de reparación requiere: Helicasas, exonucleasas, endonucleasas, polimerasas y ligasas.

Reparación directa. �Modificación de nucleótidos a su estructura original. �Ejemplo: Reparación de roturas ionizantes por la DNA Ligasa III. Por alquilación (MGMT) NO SE NECESITA LA RUPTURA DE LA CADENA PARA SU FUNCIONAMIENTO
Por escisión de bases. �Se remueve el nucleótido dañado y se resintetiza. �DNA Glucosilasa. �Endonucleasa AP.

Por escisión de nucleótidos. �Repara daños mas graves de DNA. �Todo un segmento de la cadena es reemplazado por DNA nuevo. �Parche corto (12 nucleótidos) y parche largo (29 nucleótidos). �XPA, factor de trascripción (XPB, XPC), XPF y XPG, polimerasa y factor de trascripción C.

Reparación posreplicativa. � Repara daños de doble cadena. � Reconoce errores aún después de haberse llevado a cabo la replicación. � Las proteínas mut S y mut L interaccionan con el sitio mal emparejado y una proteína mut. H rompe la cadena recién sintetizada. Alrededor del emparejamiento erróneo, las cadenas de DNA se separan con ayuda de una proteína denominada Mut. U y se estabilizan con SSB.

Reparación de bases mal apareadas. �Bases colocadas de forma incorrecta. �No se reconoce la secuencia errónea, sino el apareamiento anormal entre la cadena hija y la cadena progenitora. �La reparación se da en la cadena hija. Escinde parte del polinucleótido y llena el hueco.
Reunión de extremos no homólogos � Mecanismo de reparación directa para corregir las roturas de doble cadena DSB donde intervienen… DNA ligasa IV humana Complejo proteico de reconocimiento al daño que incluye: La actividad de una cinasa dependiente de DNA y a la proteína NBS 1. Constituye una medida desesperada que causa mutaciones puesto que los extremos rotos pueden ser unidos de manera independiente de su secuencia.
REPARACIÓN EN MITOCONDRIA �Mitocondria: Suficientemente equipada para realizar la reparación por escisión de bases (BER) para reparar el daño causado por agentes oxidantes.

RECOMBINACIÓN � Proceso que da origen al entrecruzamiento e intercambio de segmentos de DNA que ocurre entre cromosomas homólogos durante la meiosis. � Sin ella, los genomas serían estructuras estables, sufriendo muy pocos cambios y el potencial evolutivo del genoma estaría muy restringido.
- Slides: 41