Apoptose 20012002 Prof Doutor Jos Cabeda Biologia Celular

Apoptose 2001/2002 Prof. Doutor José Cabeda Biologia Celular
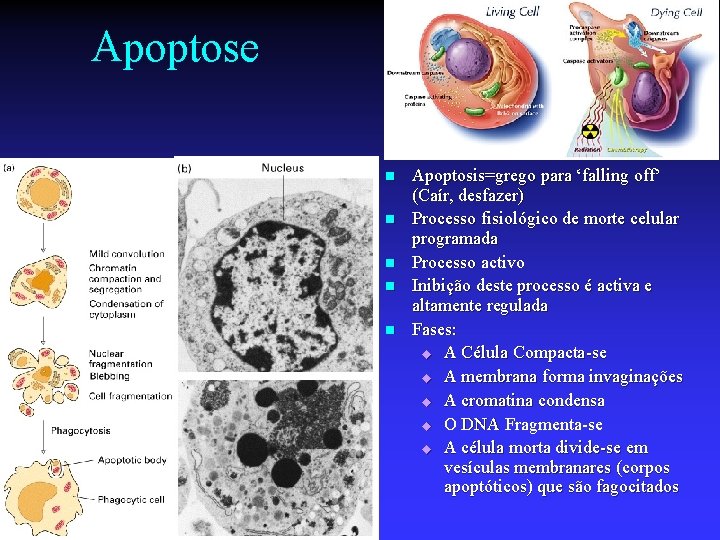
Apoptose n n n Apoptosis=grego para ‘falling off’ (Caír, desfazer) Processo fisiológico de morte celular programada Processo activo Inibição deste processo é activa e altamente regulada Fases: u A Célula Compacta-se u A membrana forma invaginações u A cromatina condensa u O DNA Fragmenta-se u A célula morta divide-se em vesículas membranares (corpos apoptóticos) que são fagocitados
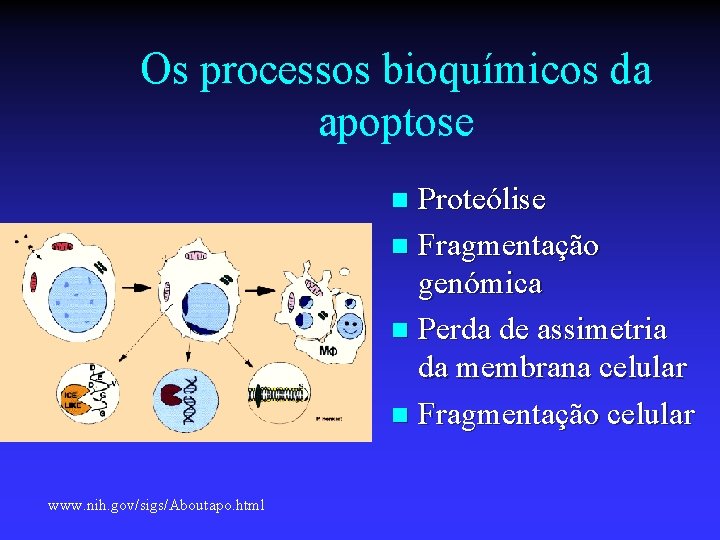
Os processos bioquímicos da apoptose Proteólise n Fragmentação genómica n Perda de assimetria da membrana celular n Fragmentação celular n www. nih. gov/sigs/Aboutapo. html

Apoptose versus Necrose n n n n Apoptose Determinada genéticamente Ocorre dentro dos intervalos fisiológicos Célula compacata-se Resulta de diversos passos intrinsecamente regulados Participa no equilibrio homeostático do organismo Fenómeno individual celular (suícidio celular) Nunca ocorre perda de estanquicidade membranar As vesículas formadas são removidas por fagocitose, num processo muito rápido que não deixa vestígios n n n n Necrose Determinada genéticamente Resulta da alteração súbita de um ou mais intervalos fisiológicos (p. H, Temperatura, [iónicas], etc) Citoplasma “incha” Resulta da inviabilização metabólica da célula Não tem funções homeostáticas Fenómeno colectivo a todas as células vizinhas Resulta na perda de estanquicidade da membrana O derramamento do fluido celular inicia processos tecidulares (inflamação) que duram horas ou dias e originam marcas duradouras (cicatrizes)

Controlo da apoptose n n n A apoptose em condições biológicas é uma resposta celular a variações subtis u no meio extracelular u Na membrana citoplasmática u No interior da célula O mesmo estímulo pode desencadear apoptose num tipo de célula, ser inócuo noutro, e desencadear a proliferação noutro A resposta de um tipo de célula a um dado estímulo pode ser variável pois depende de outros factores celulares (ex: fase de maturação) e ambientais (outros estímulos)

Funções da apoptose Moldar os tecidos na embriogénese n Eliminar células alteradas (ex. cancro) n Eliminar células que deixaram de ser necessárias (ex. Sistema Imunológico) n

Programmed Cell Death A. Form digits B. Form lumina C. Vestigal structure D. Mullerian/Wolffian E. Cull extras (neurons)* F. Cull immune system* G. Cull damaged cells* *focus of many studies

Anomalias da apoptose Malformações congénitas n Doenças Neurodegenerativas n Disfunções imunológicas n Tumores n

Apoptose em patologias n n n Cancro u Inibição da apoptose t HPV inactiva o promotor do p 53 t EBV aumenta a produção de bcl-2 t Algumas Leucemias B expressam níveis elevados de bcl-2 t Melanoma inibe a expressão de Apaf-1 t Alguns tipos de cancros do pulmão e do colon secretam uma proteína que bloqueia o Fas. L t Alguns tipos de tumores expressam níveis elevados de Fas. L induzindo apoptose nas CTL que com elas interactuam Doenças Auto-imunes u Defeitos na indução de apoptose t Defeitos na selecção celular t Dificuldade em desligar as respostas imunológicas Imunodeficiências u Excesso de apoptose t Deficiências na selecção positiva

Regulação da apoptose n Estudos em Caedorhabditis elegans permitiram identificar 4 grupos de genes: u Responsáveis por desencadear a apoptose u Genes envolvidos no processo apoptótico u Genes necessários para a fagocitose dos corpos apoptóticos u Genes necessários para a dissolução final dos corpos fagocitados bloqueio Ced-9 detonação Egl-1, ces-2 apoptose Ced-3, ced-4, ced-8, ced-11 fagocitose dissolução Ced-1, ced-2, ced-5, ced-6, ced-7, ced-10 Nuc-1
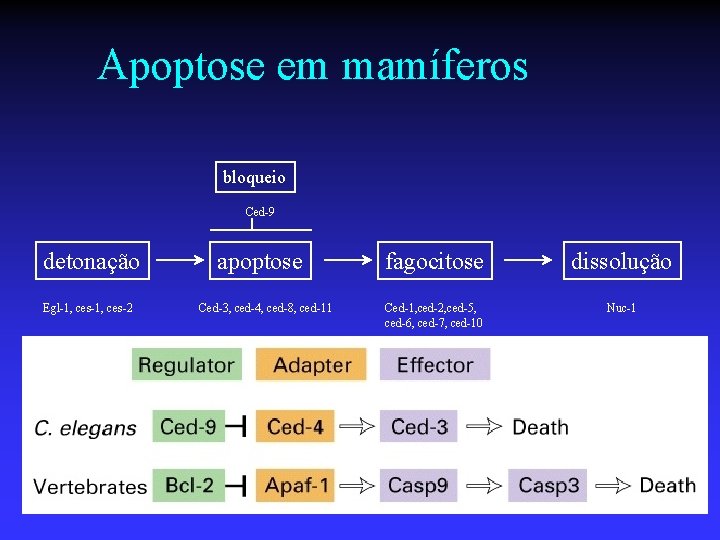
Apoptose em mamíferos bloqueio Ced-9 detonação Egl-1, ces-2 apoptose Ced-3, ced-4, ced-8, ced-11 fagocitose dissolução Ced-1, ced-2, ced-5, ced-6, ced-7, ced-10 Nuc-1
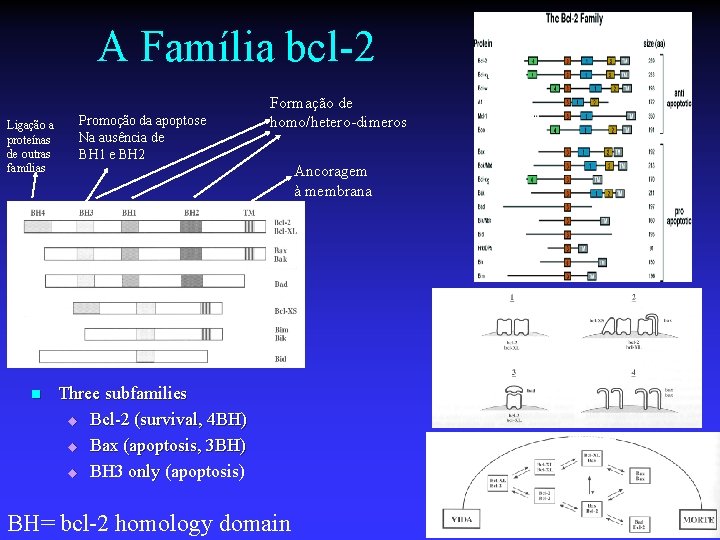
A Família bcl-2 Ligação a proteínas de outras famílias n Promoção da apoptose Na ausência de BH 1 e BH 2 Formação de homo/hetero-dimeros Ancoragem à membrana Three subfamilies u Bcl-2 (survival, 4 BH) u Bax (apoptosis, 3 BH) u BH 3 only (apoptosis) BH= bcl-2 homology domain
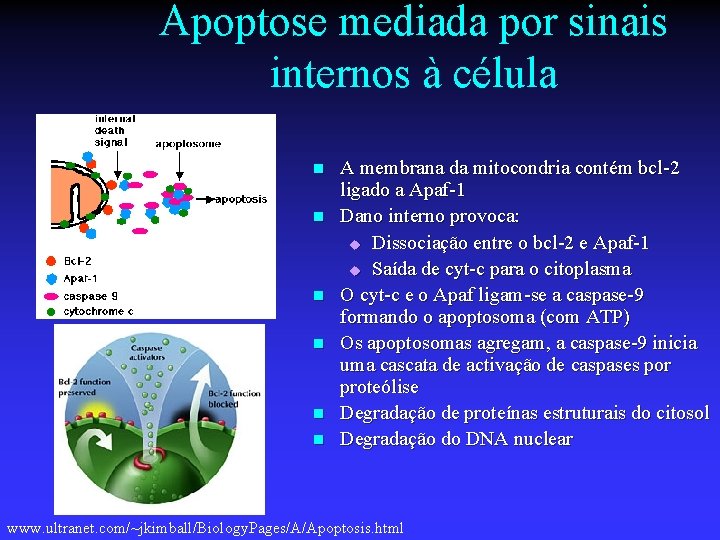
Apoptose mediada por sinais internos à célula n n n A membrana da mitocondria contém bcl-2 ligado a Apaf-1 Dano interno provoca: u Dissociação entre o bcl-2 e Apaf-1 u Saída de cyt-c para o citoplasma O cyt-c e o Apaf ligam-se a caspase-9 formando o apoptosoma (com ATP) Os apoptosomas agregam, a caspase-9 inicia uma cascata de activação de caspases por proteólise Degradação de proteínas estruturais do citosol Degradação do DNA nuclear www. ultranet. com/~jkimball/Biology. Pages/A/Apoptosis. html

Apoptose mediana por sinais externos à célula n n Fas e o receptor do TNF são proteínas de membrana constitucionais A ligação de Fas. L e TNF induz: u Activação de caspase 8 t Inicia a cascata de activação de caspases • Degradação de proteínas estruturantes • Degradação do DNA nuclear www. ultranet. com/~jkimball/Biology. Pages/A/Apoptosis. html
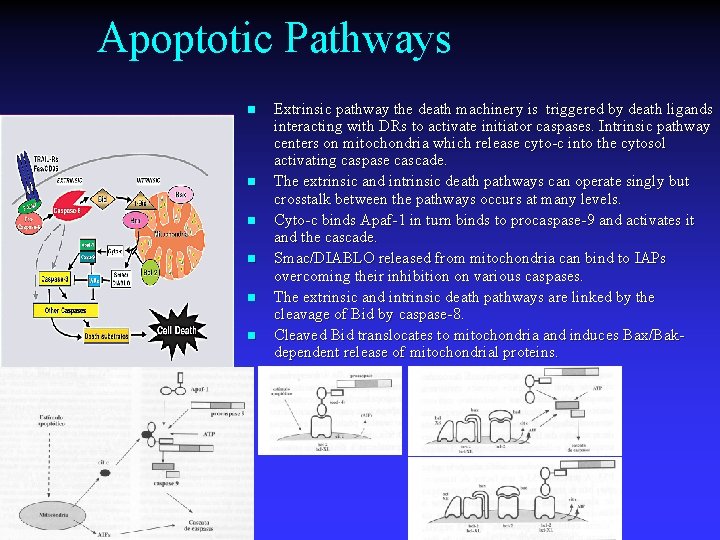
Apoptotic Pathways n n n Extrinsic pathway the death machinery is triggered by death ligands interacting with DRs to activate initiator caspases. Intrinsic pathway centers on mitochondria which release cyto-c into the cytosol activating caspase cascade. The extrinsic and intrinsic death pathways can operate singly but crosstalk between the pathways occurs at many levels. Cyto-c binds Apaf-1 in turn binds to procaspase-9 and activates it and the cascade. Smac/DIABLO released from mitochondria can bind to IAPs overcoming their inhibition on various caspases. The extrinsic and intrinsic death pathways are linked by the cleavage of Bid by caspase-8. Cleaved Bid translocates to mitochondria and induces Bax/Bakdependent release of mitochondrial proteins.

Death Receptors n n n Modular Structures u CRD=cysteine rich extracellular domain u DD=cytoplasmic death domain Adapters/FADD, etc u contain DDs to interact with receptors and transmit apoptotic signal to machinery Receptors have unique features to recognize ligand with specificity u TNFR 1/TNF-a, lymphotoxin alpha u Fas (CD 95)/Fas. L, DAXX u DR 3 & DR 4/TRAIL Not Death Receptors u Other TNF members, B & T cell antigens, lack DDs
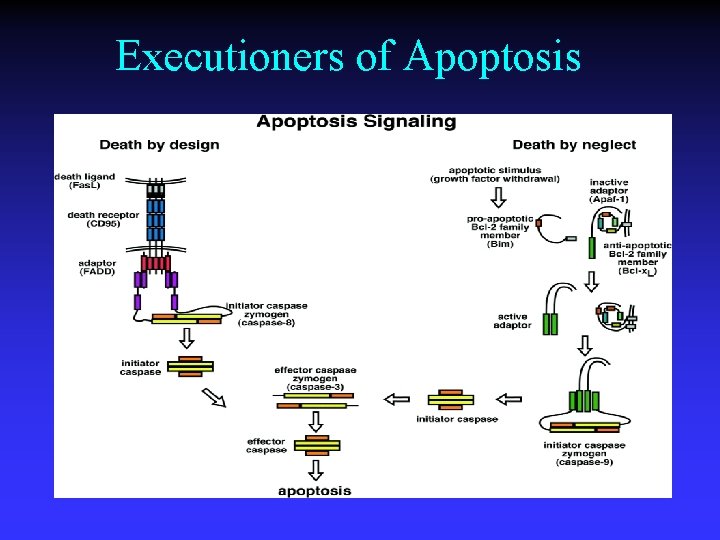
Executioners of Apoptosis

Caspases: A Common Pathway Caspases are proteases involved in 2 stages of the apoptotic pathway n Caspases are synthesized as inactive procaspases that are activated by cleavage to form the active dimer n A complex forms at the receptor that activates caspase-8 to ‘initiate’ the pathway n

Caspase Activation n Synthesized as single chain precursor Cleavage site at conserved Asp-297 N-peptide contains death-effector domain required to recruit the death receptors (DRs) to the cytosolic face
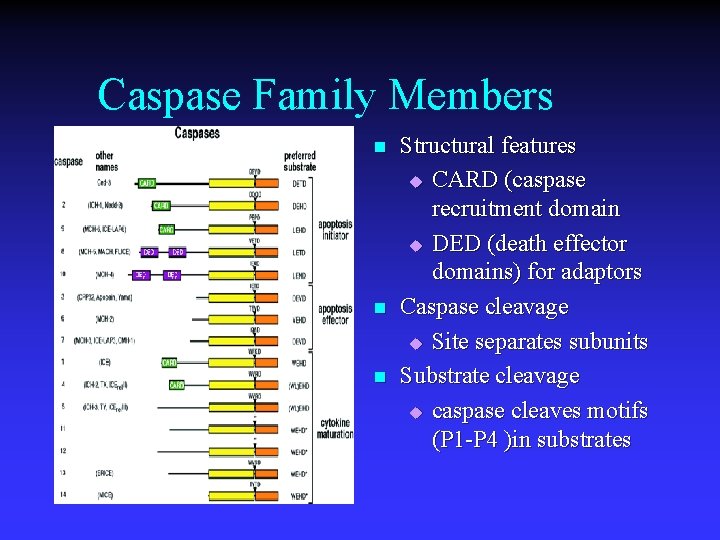
Caspase Family Members n n n Structural features u CARD (caspase recruitment domain u DED (death effector domains) for adaptors Caspase cleavage u Site separates subunits Substrate cleavage u caspase cleaves motifs (P 1 -P 4 )in substrates
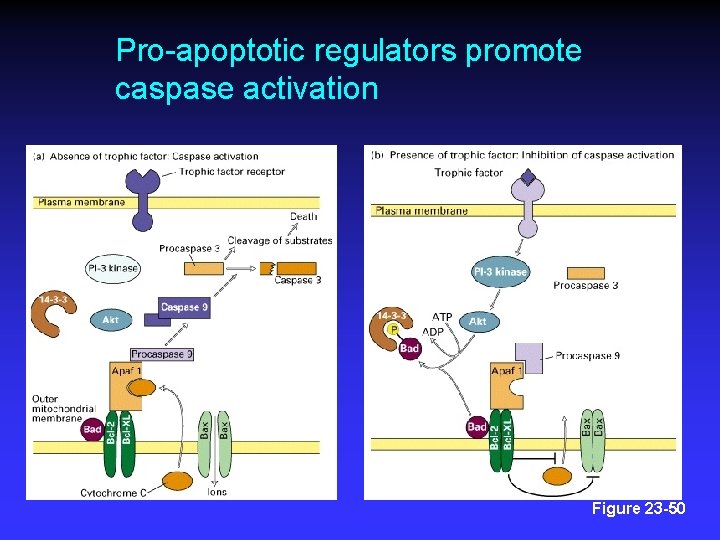
Pro-apoptotic regulators promote caspase activation Figure 23 -50
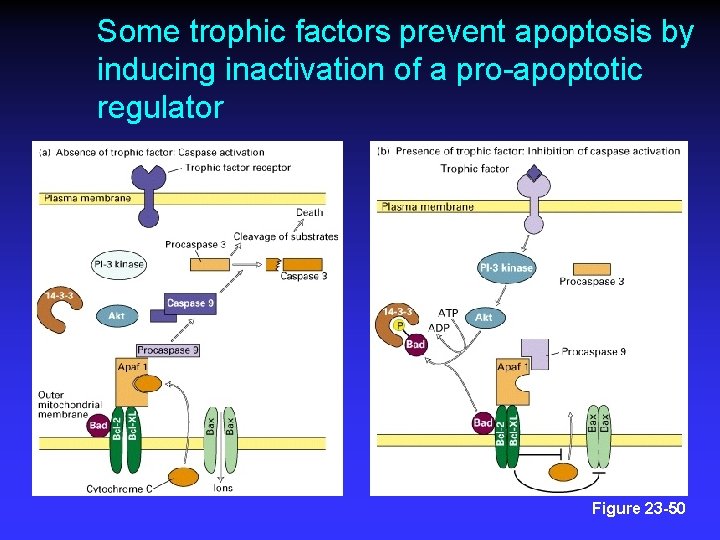
Some trophic factors prevent apoptosis by inducing inactivation of a pro-apoptotic regulator Figure 23 -50
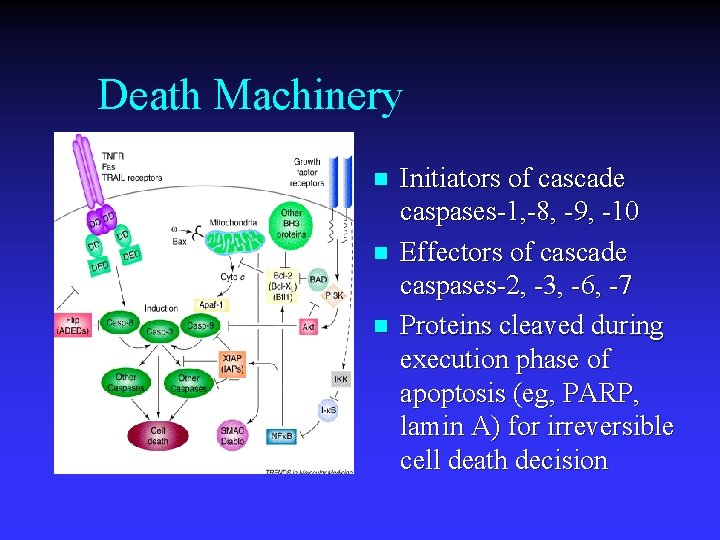
Death Machinery n n n Initiators of cascade caspases-1, -8, -9, -10 Effectors of cascade caspases-2, -3, -6, -7 Proteins cleaved during execution phase of apoptosis (eg, PARP, lamin A) for irreversible cell death decision

Cysteine Aspartate-specific Proteases Caspase Substrates Cleavage motif Caspase-1 pro-IL-1 beta YVHD-A Caspase-3 PARP DEVD-G* DNA-PK DEVD-N Rb DEAD-G Caspase-8 all other pro-caspases Caspase-9 PARP DEVD-G* procaspase-3 DEVD-G*
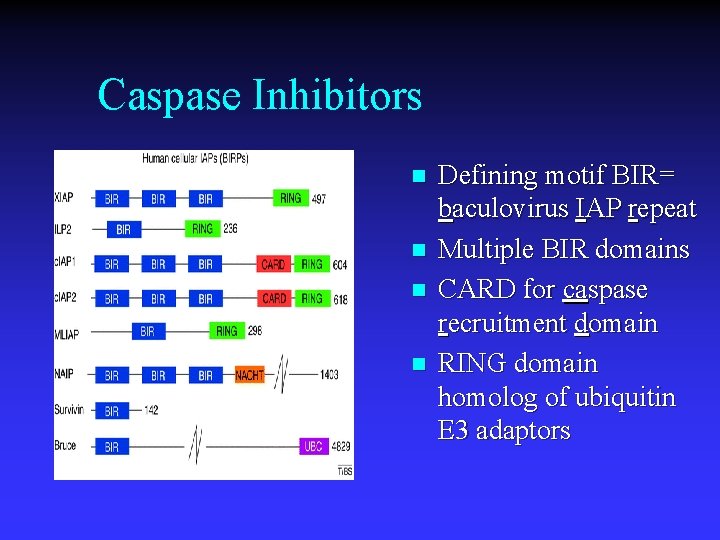
Caspase Inhibitors n n Defining motif BIR= baculovirus IAP repeat Multiple BIR domains CARD for caspase recruitment domain RING domain homolog of ubiquitin E 3 adaptors

Caspase Inhibitors n IAPs (inhibitors of apoptosis) u u n FLIPS (FLICE inhibitory proteins) u u u n BIR motif necessary/sufficient for anti-apoptotic activity XIAP, c. IAP 1, c. IAP 2 inhibit processing of procaspases-3, 6, 7 by inhibiting cytochrome-c induced activation of caspase-9 Contain 2 death effector domains (DEDS) DEDs interfere with FADD/caspase-8 interaction and activation Block early events of other death receptors (TNFR 1, TRAIL/DR 4) Peptide inhibitors u Synthetic peptide sequences based on substrate binding pocket motif in positions P 1 -P 4 (Ac-YVAD-cho, c-DEVD-cho)
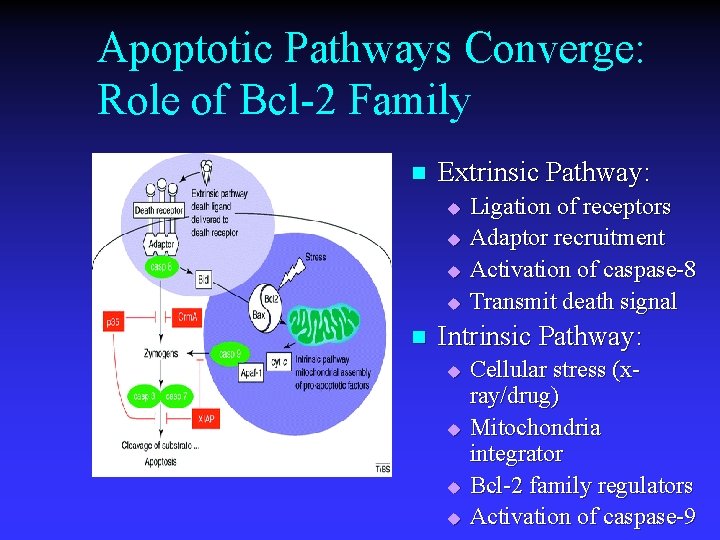
Apoptotic Pathways Converge: Role of Bcl-2 Family n Extrinsic Pathway: u u n Ligation of receptors Adaptor recruitment Activation of caspase-8 Transmit death signal Intrinsic Pathway: u u Cellular stress (xray/drug) Mitochondria integrator Bcl-2 family regulators Activation of caspase-9
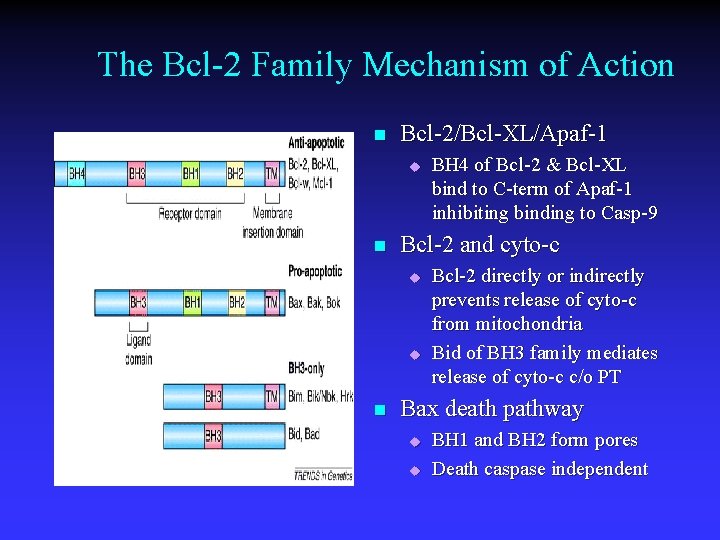
The Bcl-2 Family Mechanism of Action n Bcl-2/Bcl-XL/Apaf-1 u n Bcl-2 and cyto-c u u n BH 4 of Bcl-2 & Bcl-XL bind to C-term of Apaf-1 inhibiting binding to Casp-9 Bcl-2 directly or indirectly prevents release of cyto-c from mitochondria Bid of BH 3 family mediates release of cyto-c c/o PT Bax death pathway u u BH 1 and BH 2 form pores Death caspase independent
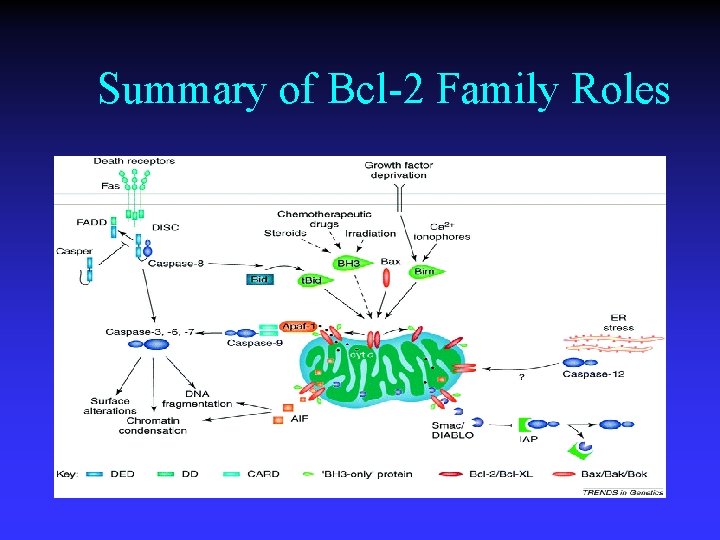
Summary of Bcl-2 Family Roles
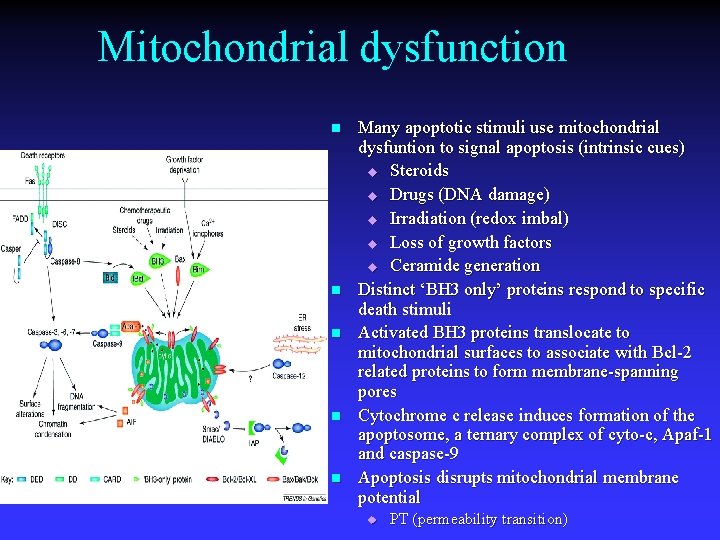
Mitochondrial dysfunction n n Many apoptotic stimuli use mitochondrial dysfuntion to signal apoptosis (intrinsic cues) u Steroids u Drugs (DNA damage) u Irradiation (redox imbal) u Loss of growth factors u Ceramide generation Distinct ‘BH 3 only’ proteins respond to specific death stimuli Activated BH 3 proteins translocate to mitochondrial surfaces to associate with Bcl-2 related proteins to form membrane-spanning pores Cytochrome c release induces formation of the apoptosome, a ternary complex of cyto-c, Apaf-1 and caspase-9 Apoptosis disrupts mitochondrial membrane potential u PT (permeability transition)

Mitochondrial Permeability Transition n Effectors of PT u Divalent cations Ca 2+ u ROS and nitric oxide u Conc of some peptides (transport signal sequens) u Lipid mediators u Any major change in energy balance (ATP, NAD) or redox state PT functions to integrate stress responses and any major damage of cells will trigger PT. PT itself causes change in energy and redox balance, when massive, can lock the cell into irreversible stage.

Permeability Transition Pore n Bcl-2 family members control PTP channel u n PTP a large pore induced by necrotic or apoptotic signals u u u n n Bcl-2 proteins in membrane of mitochondria OM, outer membrane IM, inner membrane IMS, inner membrane space PT is achieved by H+ ion gradient generated by electron transport. The H+ gradient is used by the Fo. F 1 synthase to synthesize ATP. Opening of PTP results in mitochondrial depolarization, uncoupling of oxidat phosphorylation and swelling of mitochondria Direct association between Bax and ANT or Bax and VDAC have been proposed

Role of Mitochondria in Apoptosis n n Releases pro-apoptotic molecules into cytosol upon death stimuli Apoptosome is formed (Cyto-c, Apaf-1, casp-9) Opening of PTP can release procasp-2 or -9 Bcl-2 (tethering protein) can regulate activation of mitochondrial pool

Summary of the Players n n n Death Pathways Triggering stimuli Caspases Bcl-2 family Mitochondria Death by apoptosis vs necrosis

Oncologia 2001/2002 Prof. Doutor José Cabeda Biologia Celular

CANCRO: UMA DOENÇA GENÉTICA DE CÉLULAS SOMÁTICAS n A origem genética dos tumores u u Proto-oncogenes e oncogenes Factores de crescimento t t u n n Genes de Supressão tumoral Os carcinogénios como mutagénios Agentes virais na origem dos tumores u u n Receptores para factores de crescimento Transdutores intracelulares de sinal Factores de transcrição nuclear Proteínas de controlo do ciclo celular Oncogenes virais Conversão de proto-oncogenes celulares em oncogenes Activação de proto-oncogenes Amplificação de proto-oncogene A "estatística" na origem dos tumores

Proto-oncogenes e Oncogenes n n Proto-oncogenes u Genes normais que depois de alterados por mutação originam um fenótipo tumoral u Fazem parte do património genético de todos Oncogenes u Gene resultante da alteração de um protooncogene, e que causa um fenótipo tumoral u Fazem parte do património genético das células transformadas
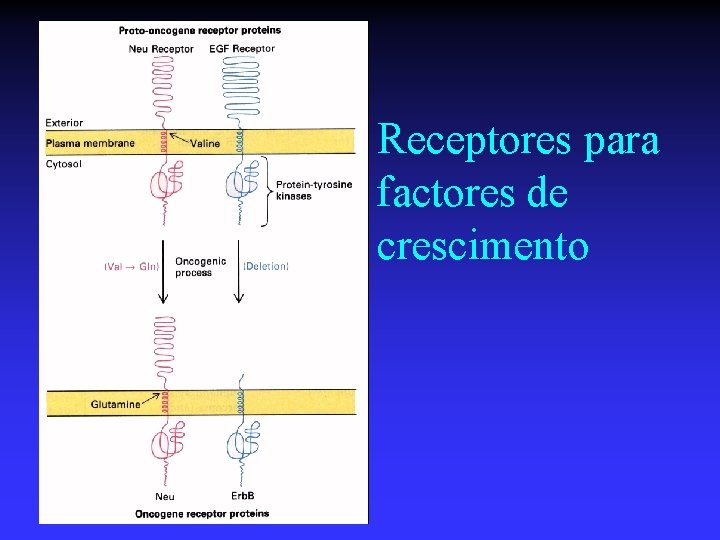
Receptores para factores de crescimento

A GENÉTICA MOLECULAR EM HEMATO-ONCOLOGIA ANOMALIAS GENÉTICAS EM HEMATOONCOLOGIA CANCRO: UMA DOENÇA GENÉTICA DE CÉLULAS SOMÁTICAS n A origem genética dos tumores u u Proto-oncogenes e oncogenes Factores de crescimento t t u n n Genes de Supressão tumoral u u u Oncogenes virais Conversão de proto-oncogenes celulares em oncogenes Activação de proto-oncogenes Amplificação de proto-oncogene A "estatística" na origem dos tumores Translocações cromossómicas em hematooncologia u u u n n Translocações envolvendo genes das Ig ou TCR translocação t(8; 14)(q 24; q 32) e o EBV A t(14; 18) - BCL 2/Ig. H Translocações que originam genes hibridos u t(9; 22) - bcr/abl t(15; 17) - pml/rar Delecções cromossómicas em hemato-oncologia Mutações pontuais em hemato-oncologia u Os carcinogénios como mutagénios Agentes virais na origem dos tumores u n Receptores para factores de crescimento Transdutores intracelulares de sinal Factores de transcrição nuclear Proteínas de controlo do ciclo celular n mutações no gene p 53 UTILIDADE CLÍNICA DA GENÉTICA MOLECULAR EM HEMATO-ONCOLOGIA n n n Aprofundamento de conhecimentos Escolha de tratamentos específicos Monitorização da doença

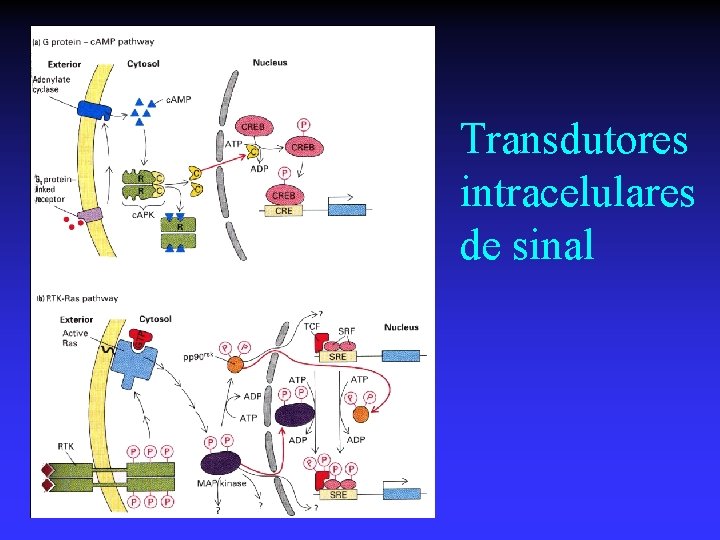
Transdutores intracelulares de sinal
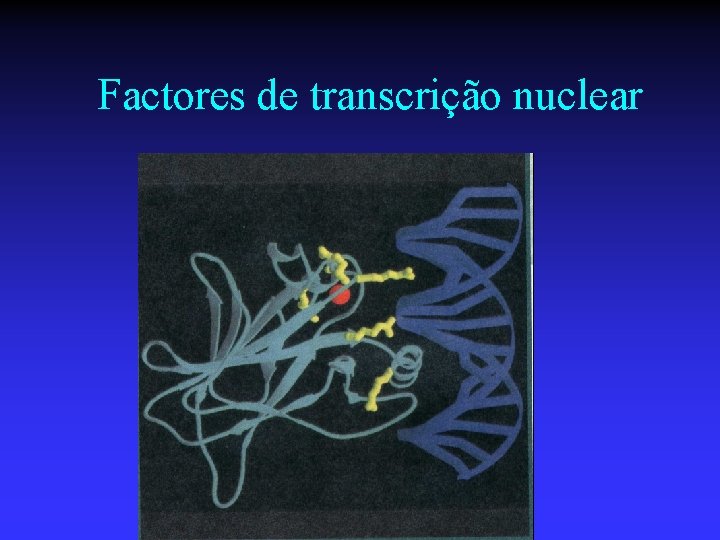
Factores de transcrição nuclear

Proteínas de controlo do ciclo celular (ciclinas) n n O ciclo celular é controlado por ciclinas (cdk), p 53 e RB (entre outros factores) u Permite uma sincronia entre o crescimento, duplicação de DNA e divisão nuclear Alterações nos genes das ciclinas podem originar fenótipo tumoral se: u Ocorrer alteração da expressão de uma ou mais ciclinas u se ocorrem mutações nas sequências codificantes dos genes que codificam as ciclinas, o p 53 ou o RB

Genes de supressão tumoral n Genes que suprimem o desenvolvimento de tumores u Mutações germinais associadas com predisposição tumoral u Fenótipo dominante, mas recessivo ao nível celular (a >parte) t O fenótipo depende da inactivação da cópia normal do gene (ex. Retinoblastoma-gene RB, um regulador do ciclo celular) u Fenótipo dominante (casos raros) t O p 53 é um estimulador da apoptose que funciona como tetrâmero. Uma diminuição da concentração

Os carcinogéneos como mutagéneos n Os mutagéneos são substâncias capazes de se interagirem com os ácidos nucleicos, modificnadolhes propriedades n Se as alterações genéticas resultantes ocorrerem em proto-oncogenes, genes de factores de crescimento, ou genes de supressão tumoral, o genótipo resultante pode ser tumoral
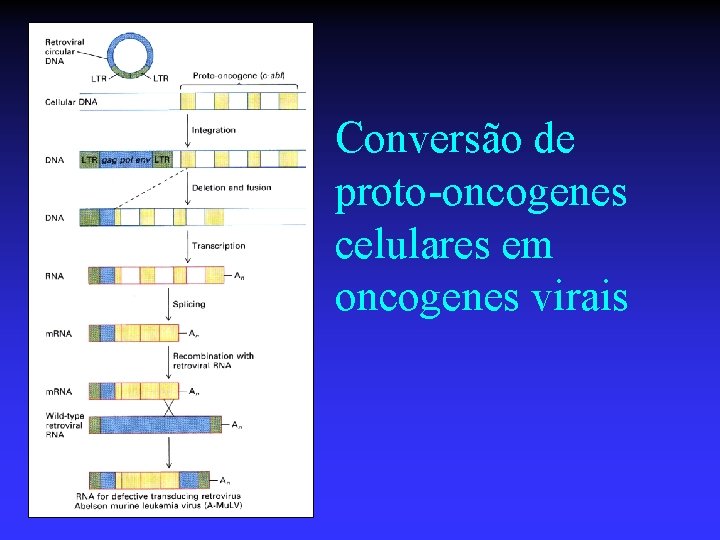
Conversão de proto-oncogenes celulares em oncogenes virais

Oncogenes virais
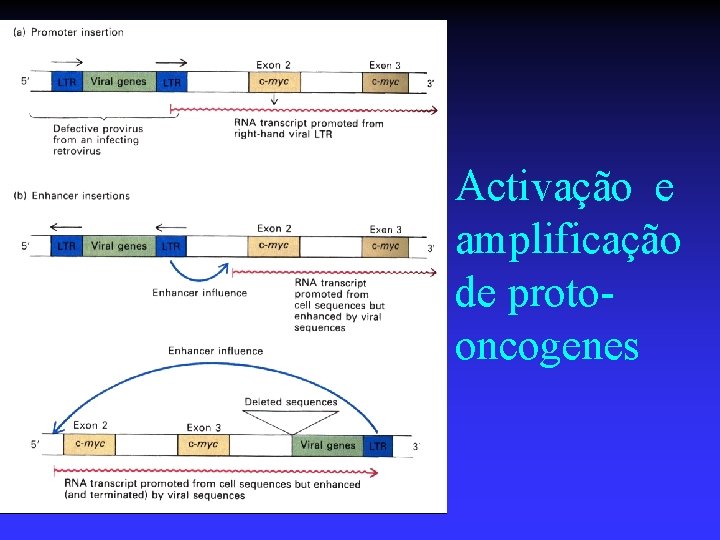
Activação e amplificação de protooncogenes

Translocações envolvendo os genes TCR e Ig
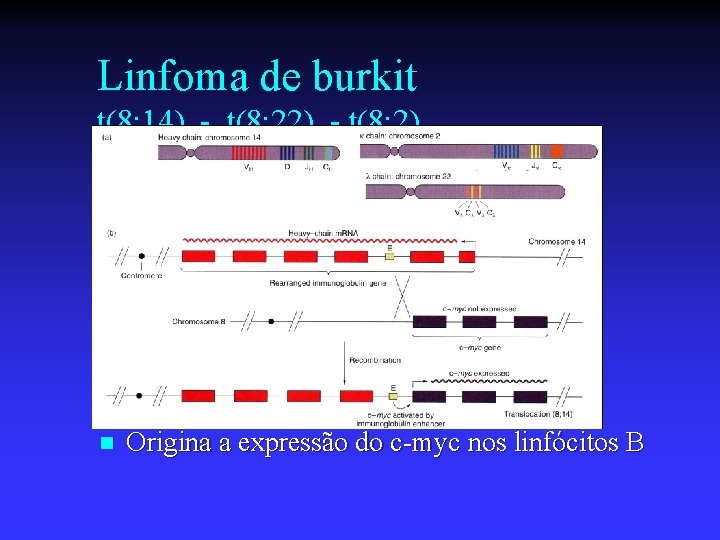
Linfoma de burkit t(8; 14) - t(8; 22) - t(8; 2) n Origina a expressão do c-myc nos linfócitos B

Linfomas foliculares e difusos Diagrama mostrando os cromossomas 14 e 18 normais, e os cromossomas resultantes da translocação t(14; 18)(q 32; q 21), envolvendo os genes BCL-2 (18 q 21) e Ig. H (14 q 32).

Genes hibridos resultantes de translocções
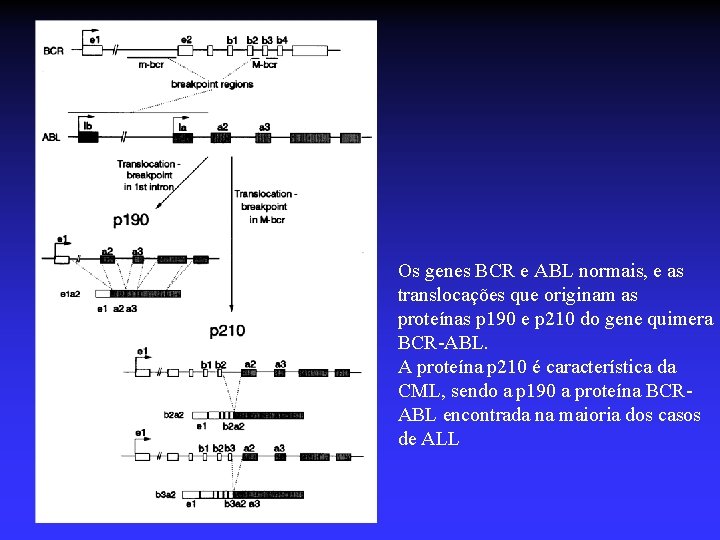
Bcr/abl Os genes BCR e ABL normais, e as translocações que originam as proteínas p 190 e p 210 do gene quimera BCR-ABL. A proteína p 210 é característica da CML, sendo a p 190 a proteína BCRABL encontrada na maioria dos casos de ALL
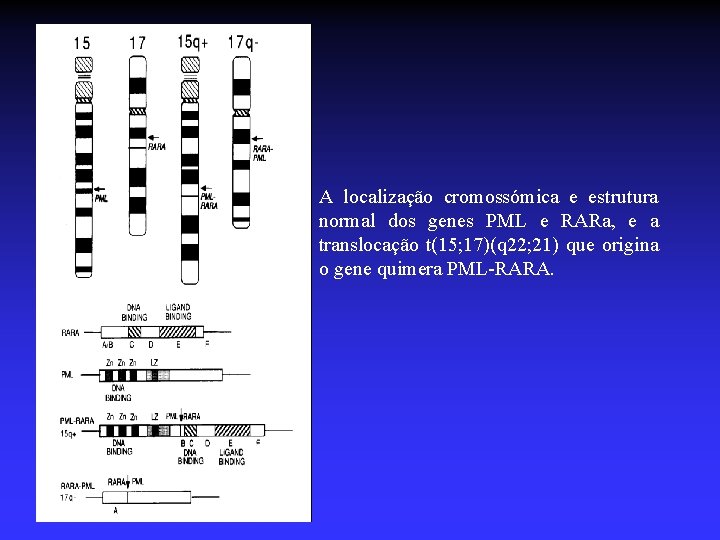
pml/rar A localização cromossómica e estrutura normal dos genes PML e RARa, e a translocação t(15; 17)(q 22; 21) que origina o gene quimera PML-RARA.
- Slides: 54