Alinhamento de Sequncias Andr Torres IOCFiocruz Laboratrio de

Alinhamento de Sequências André Torres – IOC/Fiocruz Laboratório de Biologia Computacional e Sistemas E-mail: andretorresrj@gmail. com Tópicos em Bioinformática || Alinhamento de sequencias

Tópicos principais da aula • Diferenças entre procariotos e eucariotos; • Composição das sequencias; • Código genético; • Passo a passo de um alinhamento; • Alinhamento global vs alinhamento local; • Aplicabilidade; • Softwares disponíveis. Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
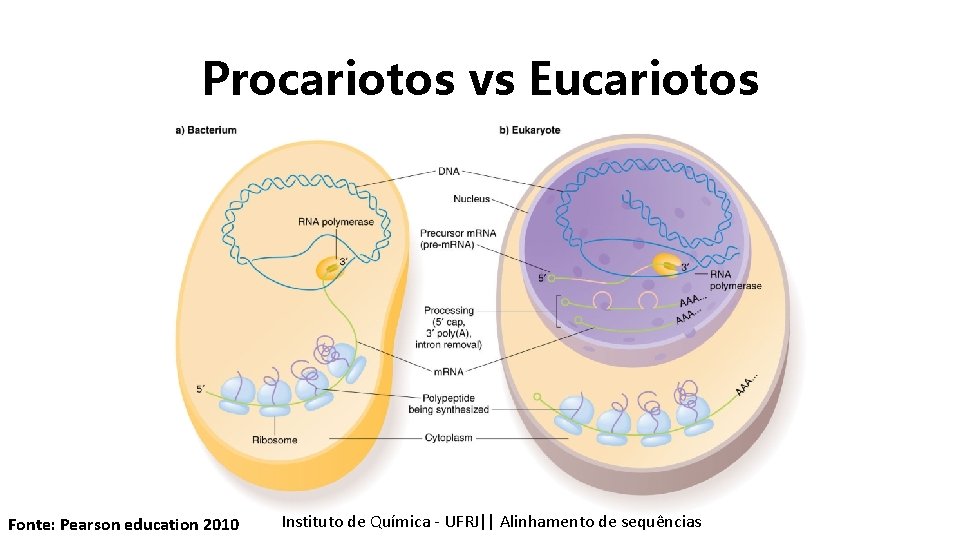
Procariotos vs Eucariotos Fonte: Pearson education 2010 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
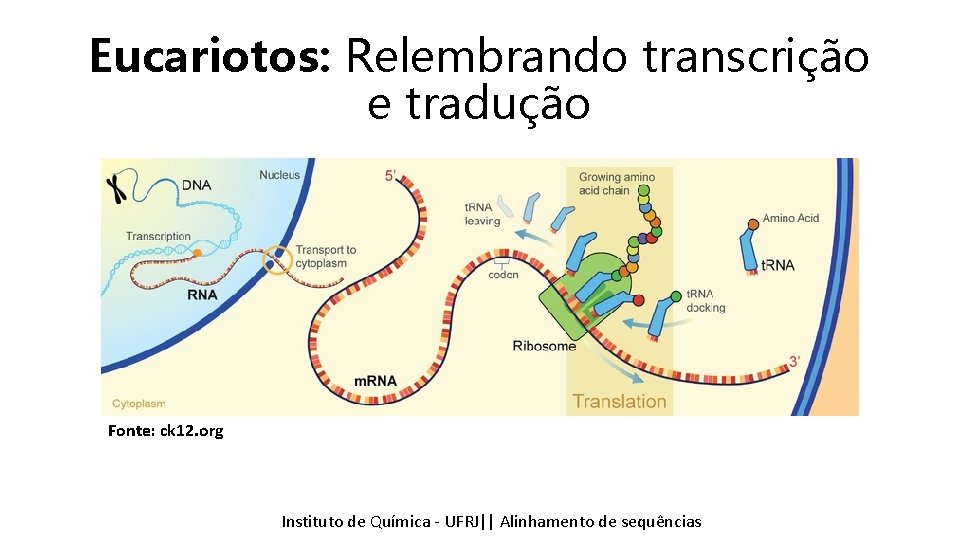
Eucariotos: Relembrando transcrição e tradução Fonte: ck 12. org Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
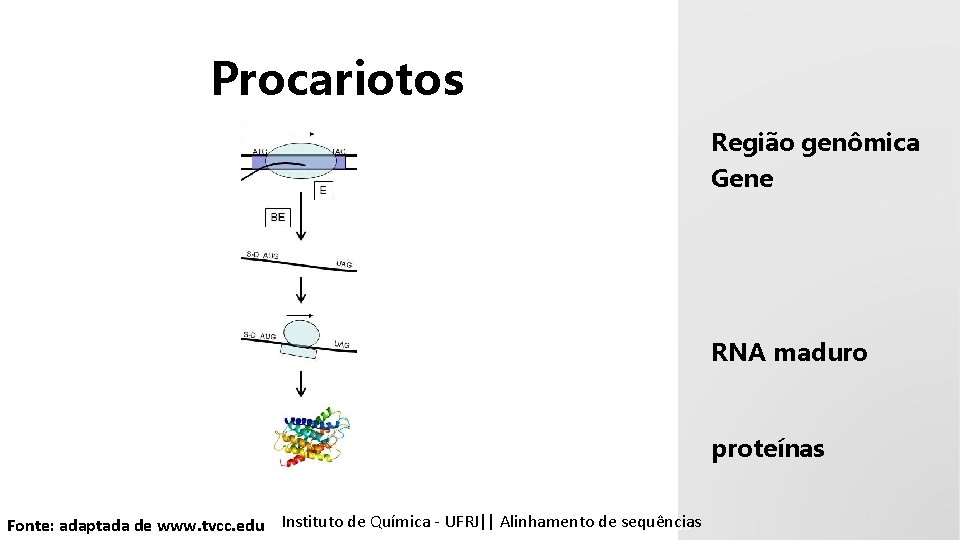
Procariotos Região genômica Gene RNA maduro proteínas Instituto Química - UFRJ|| Alinhamentodedesequencias sequências emde Bioinformática || Alinhamento Fonte: adaptada de www. tvcc. edu Tópicos
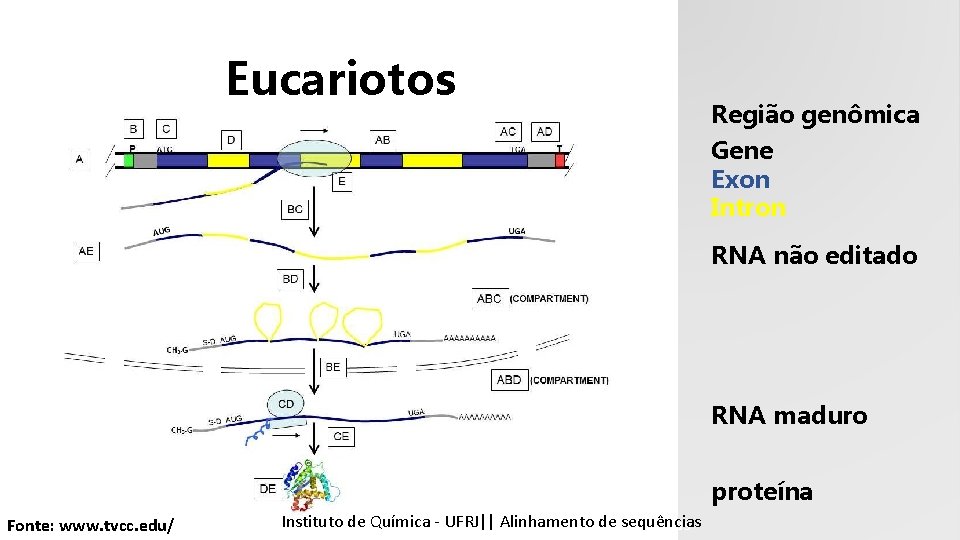
Eucariotos Região genômica Gene Exon Intron RNA não editado RNA maduro proteína Fonte: www. tvcc. edu/ Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Principais tipos de sequências DNA RNA Proteína Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
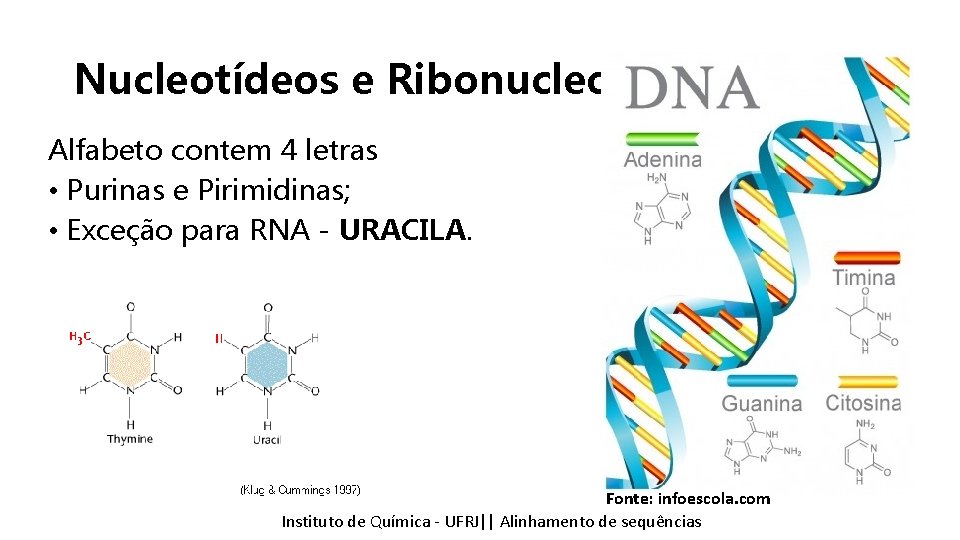
Nucleotídeos e Ribonucleotídeos Alfabeto contem 4 letras • Purinas e Pirimidinas; • Exceção para RNA - URACILA. Fonte: infoescola. com Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Proteínas são constituídas por aminoácidos 20 aminoácidos Podem ser AGRUPADOS de acordo com suas características físico. Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Proteínas são constituídas por aminoácidos Fonte: compoundchem. com

Relação entre DNA, RNA e Proteína Como a informação é mantida desde o DNA até a proteína? Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Relação entre DNA, RNA e Proteína Como a informação é mantida desde o DNA até a proteína? Porque existe um código de tradução Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Relação entre DNA, RNA e Proteína Como a informação é mantida desde o DNA até a proteína? Porque existe um código de tradução Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
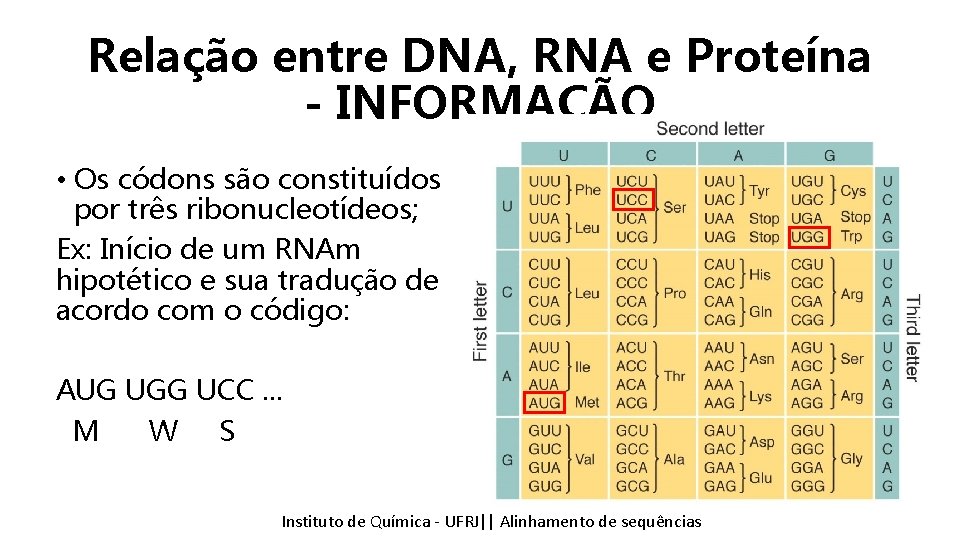
Relação entre DNA, RNA e Proteína - INFORMAÇÃO • Os códons são constituídos por três ribonucleotídeos; Ex: Início de um RNAm hipotético e sua tradução de acordo com o código: AUG UGG UCC. . . M W S Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
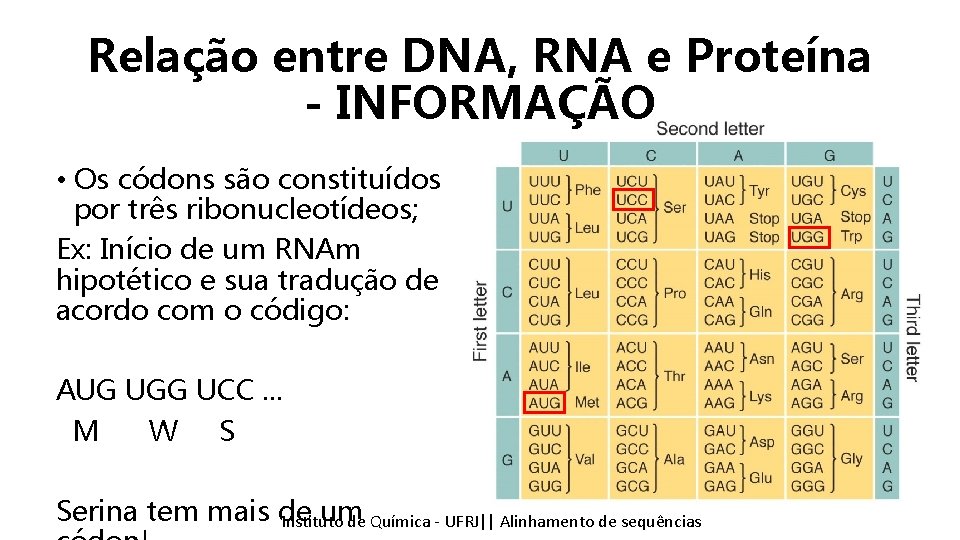
Relação entre DNA, RNA e Proteína - INFORMAÇÃO • Os códons são constituídos por três ribonucleotídeos; Ex: Início de um RNAm hipotético e sua tradução de acordo com o código: AUG UGG UCC. . . M W S Serina tem mais. Tópicos de um Instituto Química - UFRJ|| Alinhamentodedesequencias sequências emde Bioinformática || Alinhamento

Relação entre DNA, RNA e Proteína - INFORMAÇÃO Código genético é degenerado! Quantos códons codificam o aminoácido Serina? Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
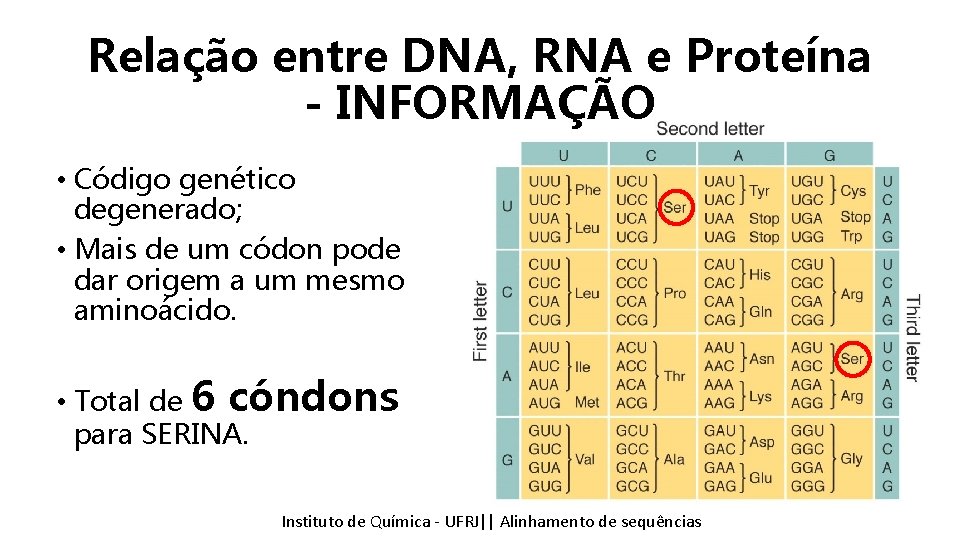
Relação entre DNA, RNA e Proteína - INFORMAÇÃO • Código genético degenerado; • Mais de um códon pode dar origem a um mesmo aminoácido. • Total de 6 cóndons para SERINA. Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

O que é alinhamento de sequências? Encontrar o melhor pareamento entre as duas ou mais sequências. Exemplo Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
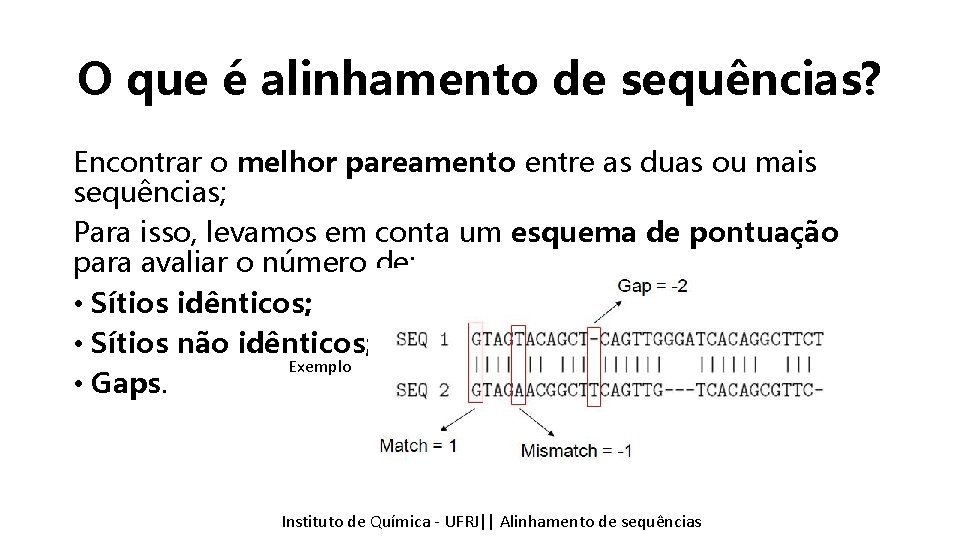
O que é alinhamento de sequências? Encontrar o melhor pareamento entre as duas ou mais sequências; Para isso, levamos em conta um esquema de pontuação para avaliar o número de: • Sítios idênticos; • Sítios não idênticos; Exemplo • Gaps. Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Problemas e limitações • Qualquer duas sequências podem ser alinhadas; • O alinhamento precisa ter um SCORE para “ranquear” qual é o melhor; • Podem existir mais de uma possibilidade de alinhamento. ACGTACGTACGTACGTACGTACGTACGT | | | | GATCGATCGATCGATCGATCGATCGATC Questão: Qual deles é o melhor? ACGTACGTACGTACGT | | | | GATCGATCGATCGATC ACGTACGTACGTACGT | | | GATCGATCGATCGATC Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Passos para o alinhamento • Como alinhar? • Como os algoritmos básicos funcionam? Vamos ver isso agora para o ALGORITMO DE NEEDLEMAN-WUNSCH e depois passar para exemplos práticos. Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Passos para o alinhamento • Vamos alinhar duas pequenas sequências hipotéticas: • Sequência 1: ATCG • Sequência 2: TCG • Vamos considerar as pontuações: • Identidade: +1 • Dissimilaridade: -1 • Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
1º passo – Construção da matriz de similaridade (dot plot) G C T A - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) Sempre começamos com um GAP G C T A - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
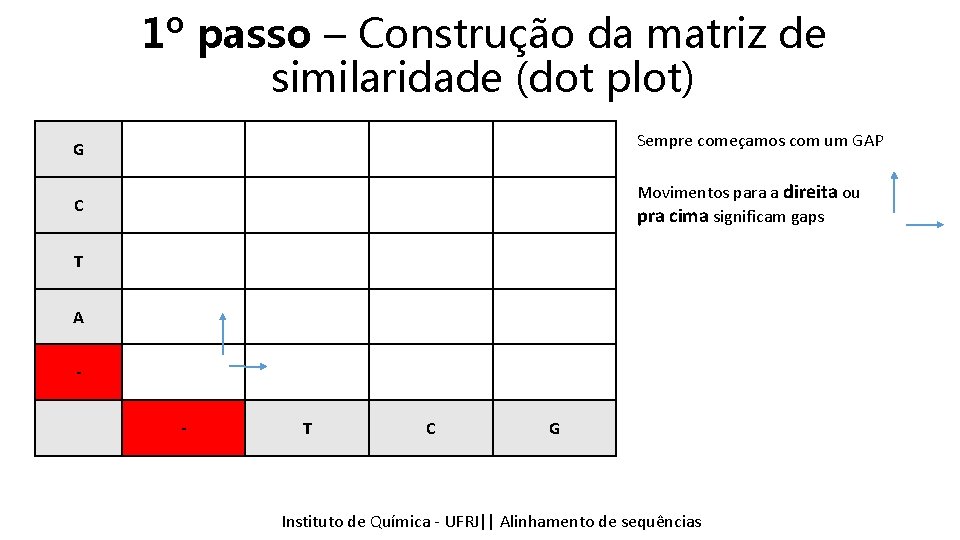
1º passo – Construção da matriz de similaridade (dot plot) G Sempre começamos com um GAP C Movimentos para a direita ou pra cima significam gaps T A - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
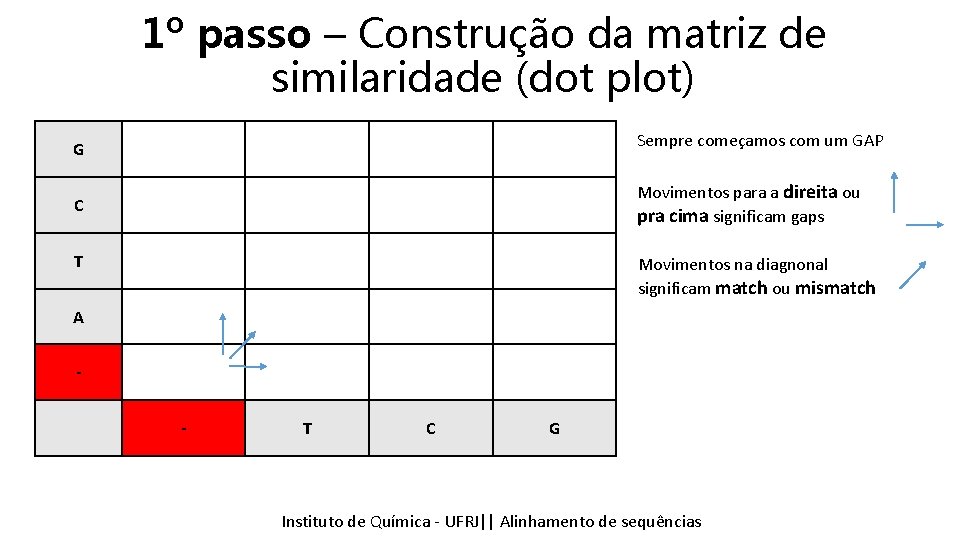
1º passo – Construção da matriz de similaridade (dot plot) G Sempre começamos com um GAP C Movimentos para a direita ou pra cima significam gaps T Movimentos na diagnonal significam match ou mismatch A - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
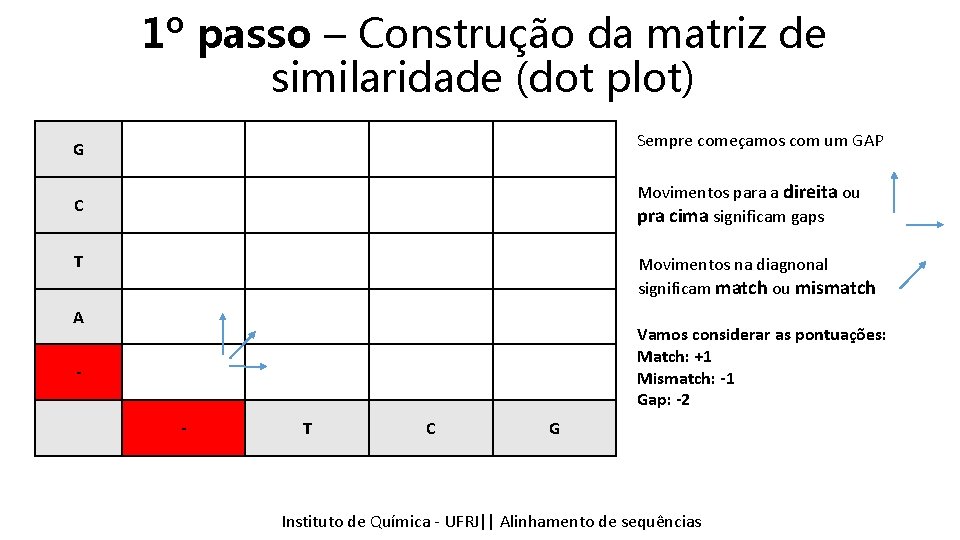
1º passo – Construção da matriz de similaridade (dot plot) G Sempre começamos com um GAP C Movimentos para a direita ou pra cima significam gaps T Movimentos na diagnonal significam match ou mismatch A Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
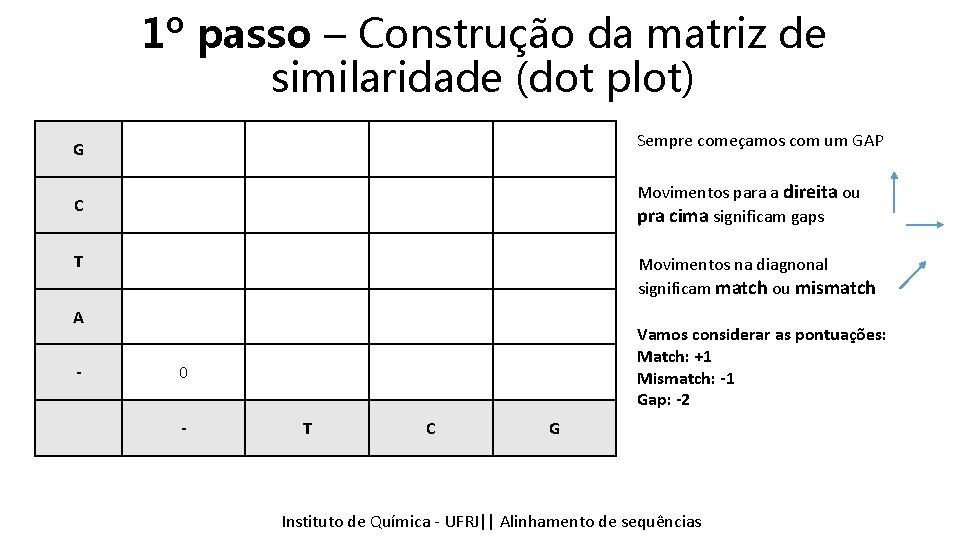
1º passo – Construção da matriz de similaridade (dot plot) G Sempre começamos com um GAP C Movimentos para a direita ou pra cima significam gaps T Movimentos na diagnonal significam match ou mismatch A - Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 0 - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G Sempre começamos com um GAP C Movimentos para a direita ou pra cima significam gaps T Movimentos na diagnonal significam match ou mismatch A -2 - 0 -2 - T Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
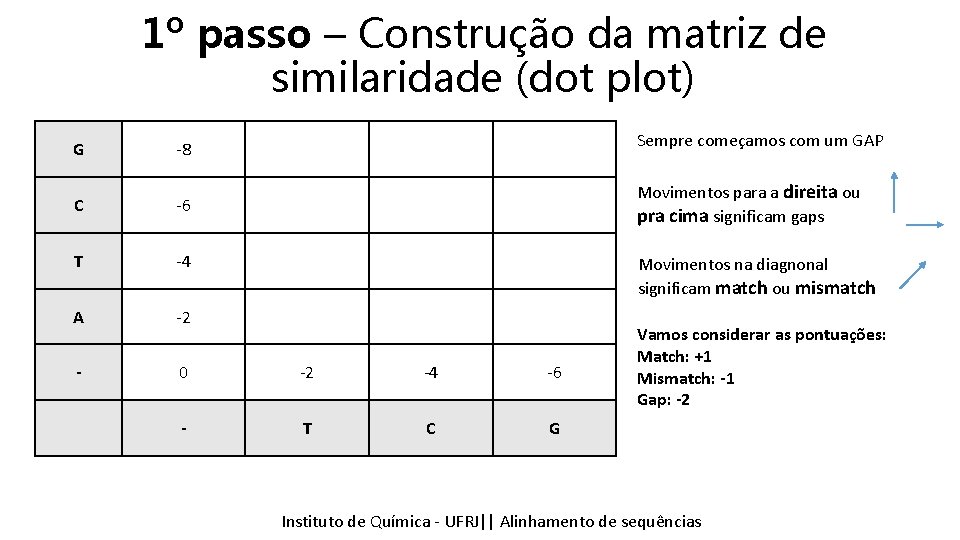
1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 A -2 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
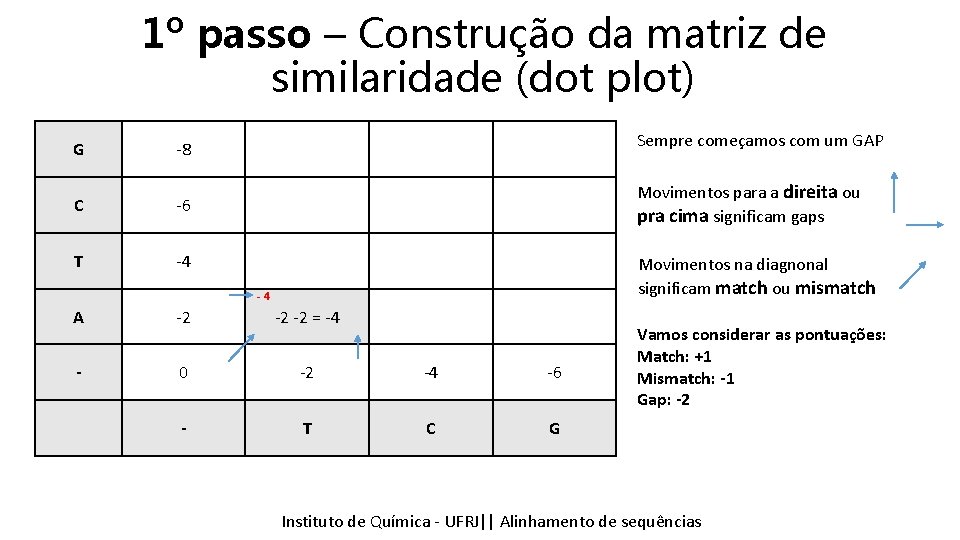
1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 Movimentos na diagnonal significam match ou mismatch -4 A -2 -2 -2 = -4 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
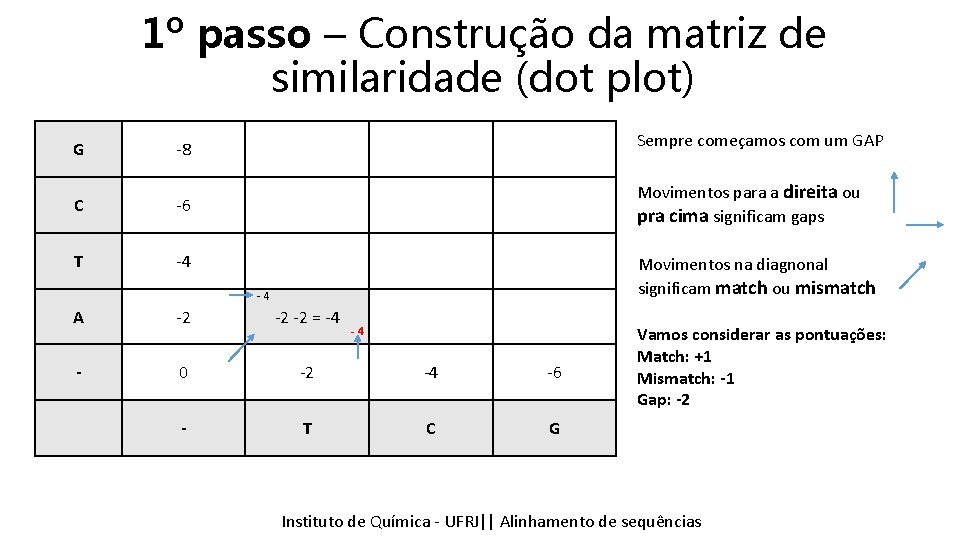
1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 Movimentos na diagnonal significam match ou mismatch -4 A -2 -2 -2 = -4 - 0 -2 -4 -6 - T C G -4 Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 Movimentos na diagnonal significam match ou mismatch -4 A -2 0 – 1 = -1 -1 - -4 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 A -2 Movimentos na diagnonal significam match ou mismatch -1 -1 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 A -2 Movimentos na diagnonal significam match ou mismatch -1 -1 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
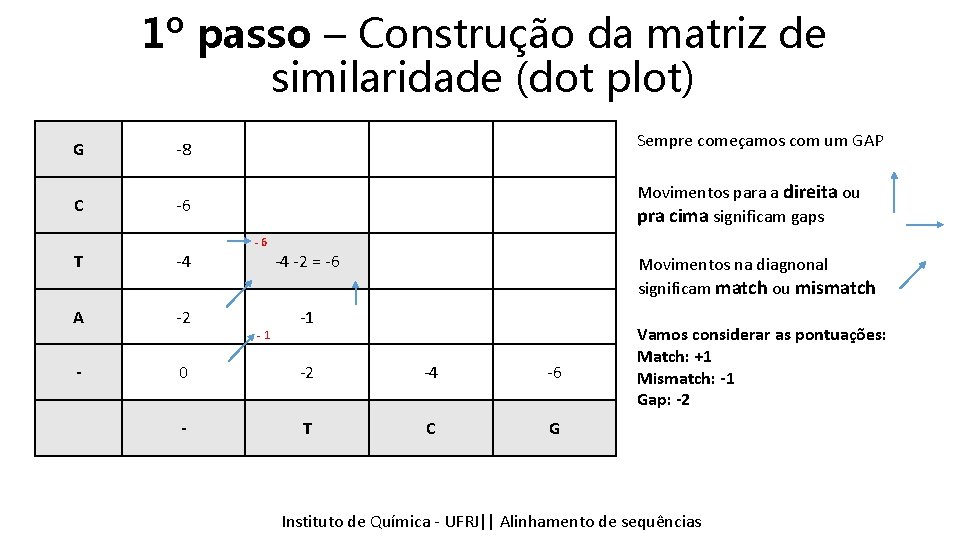
1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps -6 T -4 -4 -2 = -6 A -2 -1 Movimentos na diagnonal significam match ou mismatch -1 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
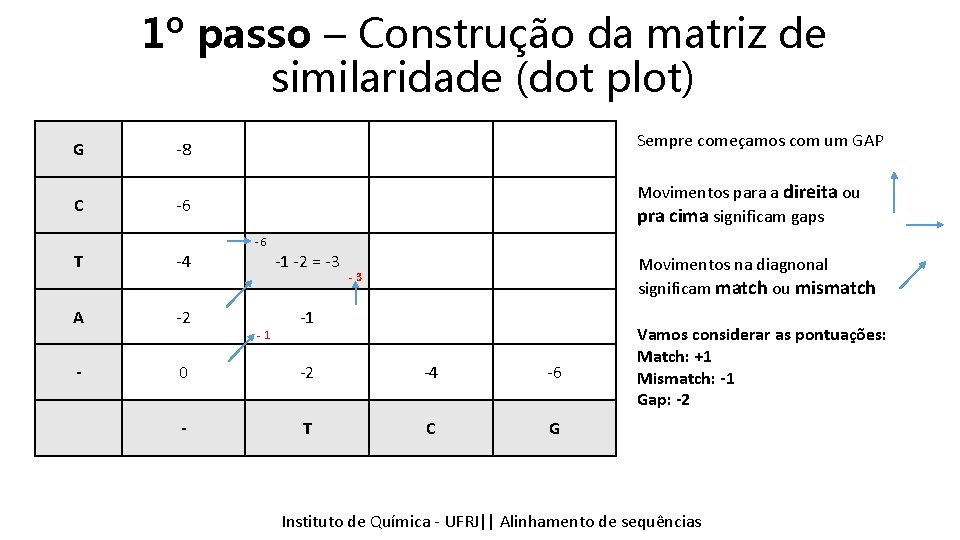
1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps -6 T -4 -1 -2 = -3 A -2 -1 Movimentos na diagnonal significam match ou mismatch -3 -1 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps -6 T -4 -2 +1 = -1 -1 A -2 Movimentos na diagnonal significam match ou mismatch -3 -1 -1 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps T -4 -1 Movimentos na diagnonal significam match ou mismatch -1 A -2 -1 -1 - 0 -2 -4 -6 - T C G Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

1º passo – Construção da matriz de similaridade (dot plot) G -8 Sempre começamos com um GAP C -6 Movimentos para a direita ou pra cima significam gaps -4 -1 Movimentos na diagnonal Seguindo essa lógica completamos significam match ou mismatch A -2 todas -1 as células da matriz. Vamos considerar as pontuações: T -1 -1 - 0 -2 -4 -6 - T C G Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
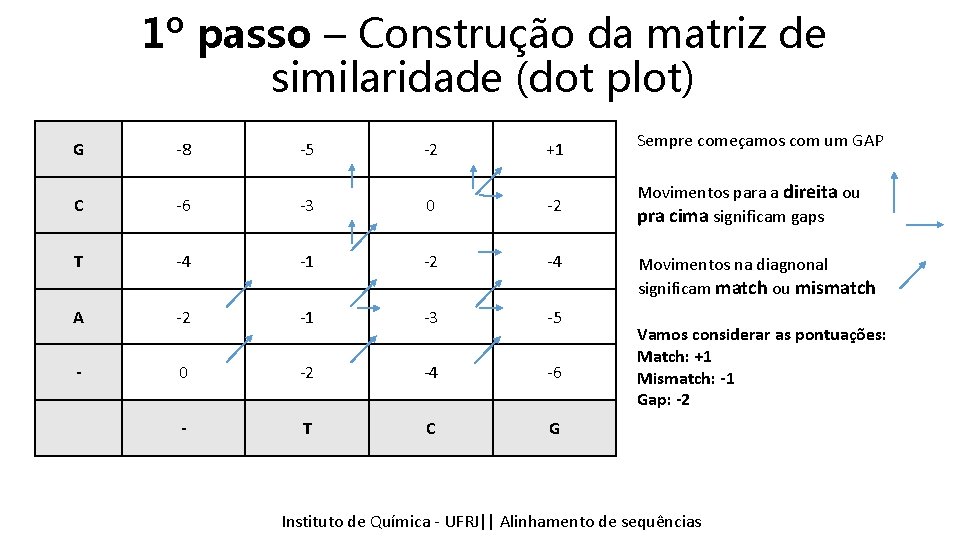
1º passo – Construção da matriz de similaridade (dot plot) G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps T -4 -1 -2 -4 A -2 -1 -3 -5 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

2º passo – Trace back G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps Agora vamos refazer o melhor caminho de T -4 -1 -2 -4 Movimentos na diagnonal significam match ou mismatch volta. A -2 -1 -3 -5 Vamos considerar as pontuações: Chamado em inglês de trace back Match: +1 0 -2 -4 -6 Mismatch: -1 Gap: -2 - T C G Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
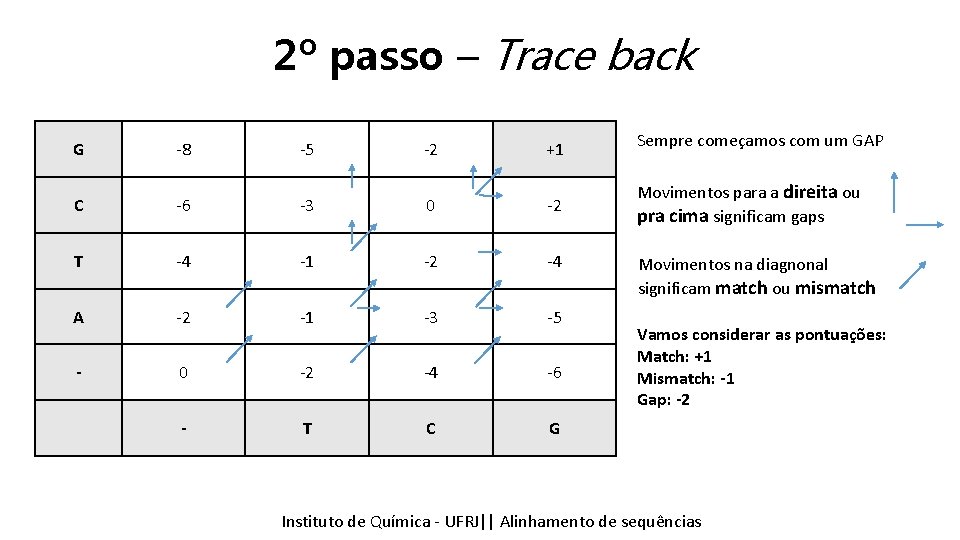
2º passo – Trace back G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps T -4 -1 -2 -4 A -2 -1 -3 -5 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
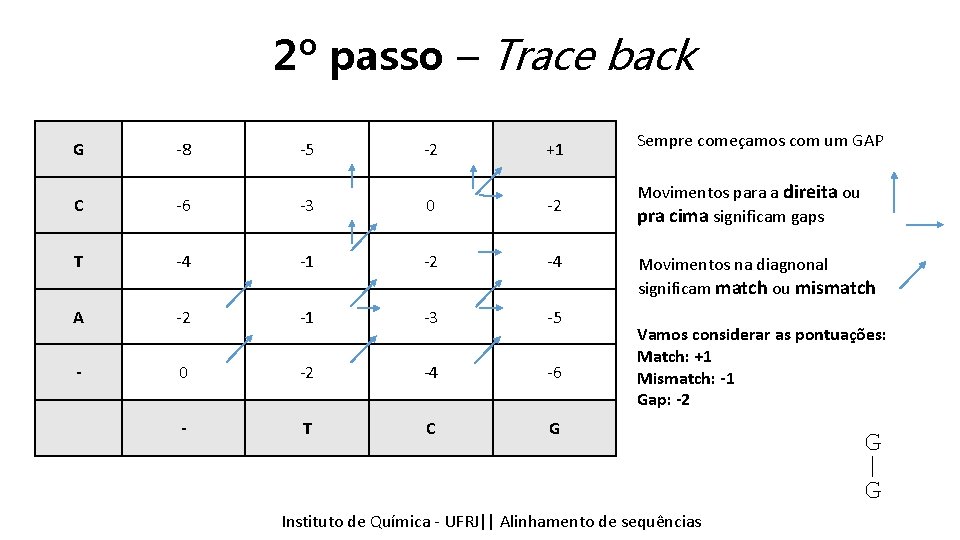
2º passo – Trace back G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps T -4 -1 -2 -4 A -2 -1 -3 -5 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento ATCG |||| _TCG
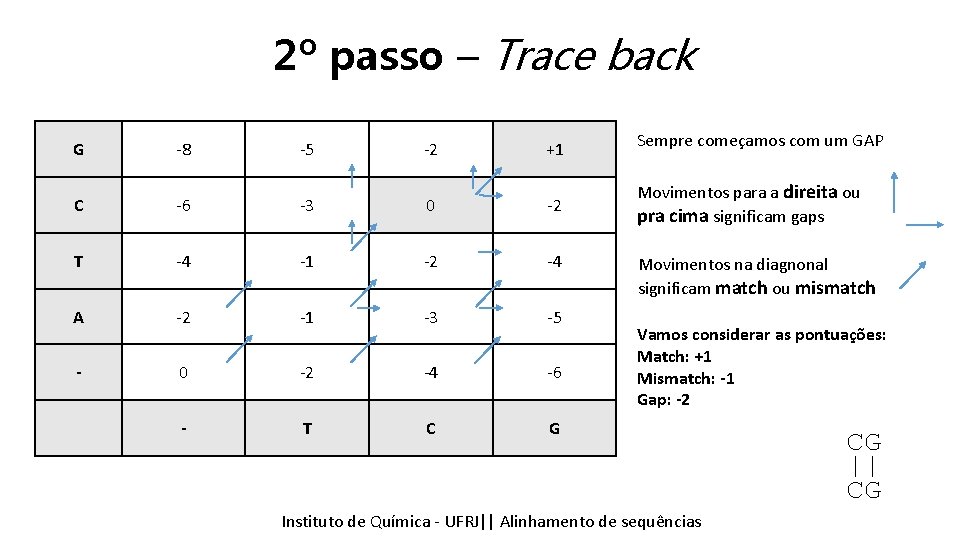
2º passo – Trace back G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps T -4 -1 -2 -4 A -2 -1 -3 -5 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento ATCG |||| _TCG
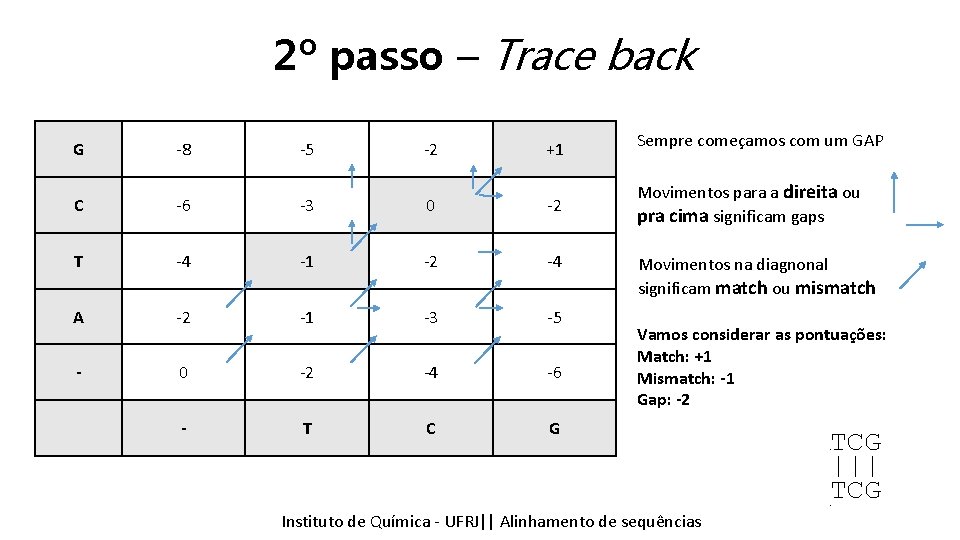
2º passo – Trace back G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps T -4 -1 -2 -4 A -2 -1 -3 -5 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento ATCG |||| _TCG
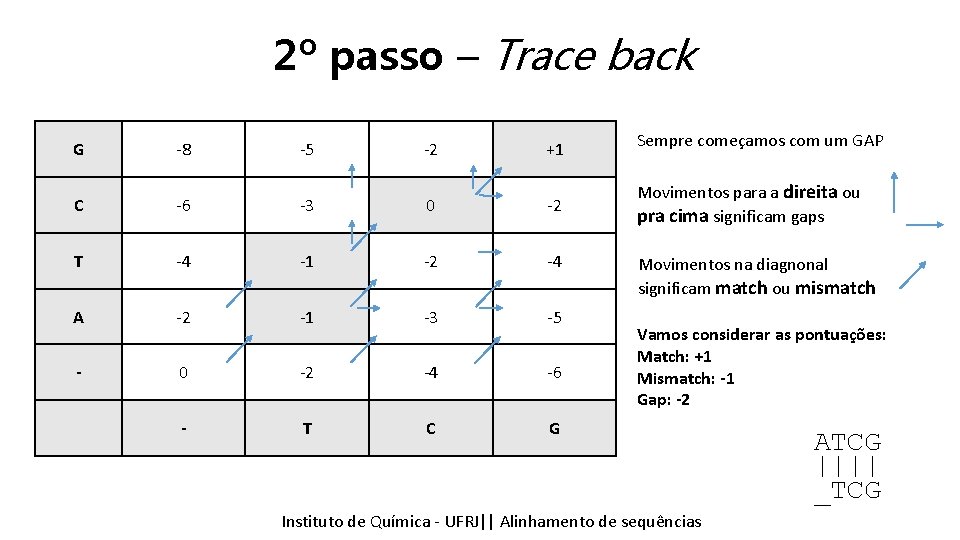
2º passo – Trace back G -8 -5 -2 +1 Sempre começamos com um GAP C -6 -3 0 -2 Movimentos para a direita ou pra cima significam gaps T -4 -1 -2 -4 A -2 -1 -3 -5 - 0 -2 -4 -6 - T C G Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento ATCG |||| _TCG
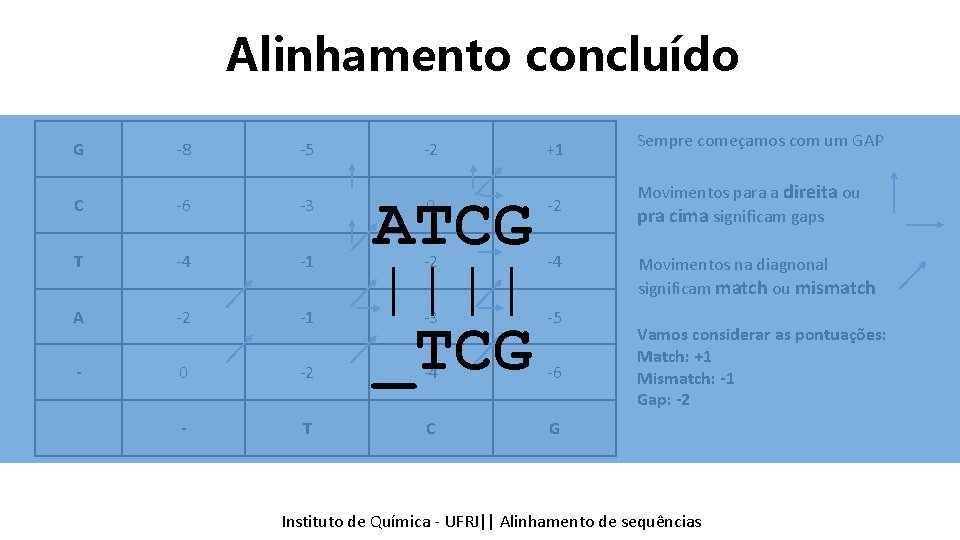
Alinhamento concluído G -8 -5 C -6 -3 T -4 -1 A -2 -1 - 0 -2 - T +1 Sempre começamos com um GAP 0 -2 Movimentos para a direita ou pra cima significam gaps -2 -4 -3 -5 -4 -6 C G -2 ATCG |||| _TCG Movimentos na diagnonal significam match ou mismatch Vamos considerar as pontuações: Match: +1 Mismatch: -1 Gap: -2 Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
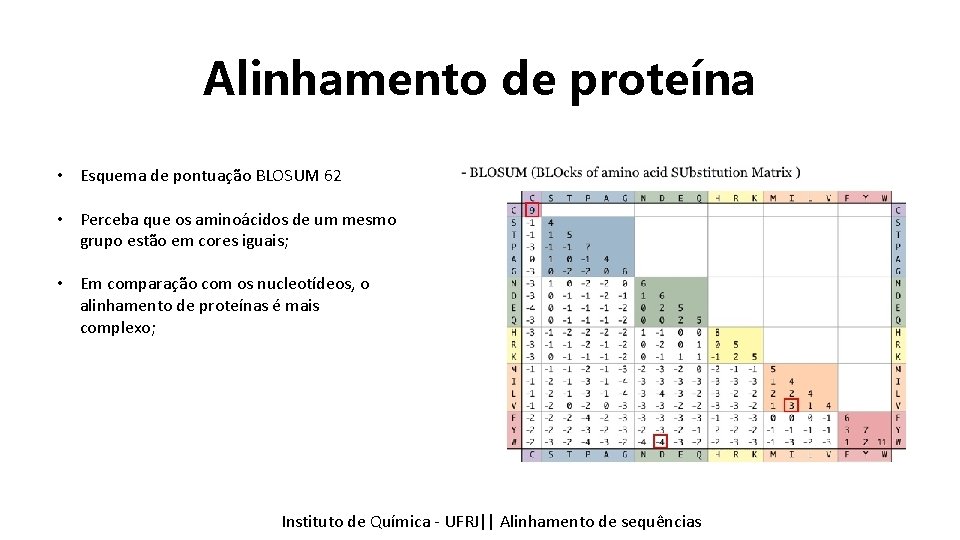
Alinhamento de proteína • Esquema de pontuação BLOSUM 62 • Perceba que os aminoácidos de um mesmo grupo estão em cores iguais; • Em comparação com os nucleotídeos, o alinhamento de proteínas é mais complexo; Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento
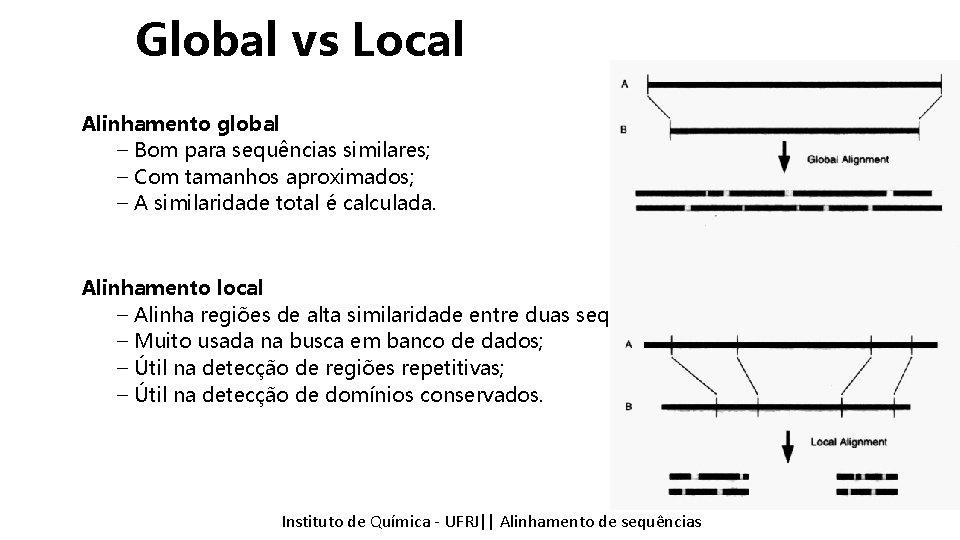
Global vs Local Alinhamento global – Bom para sequências similares; – Com tamanhos aproximados; – A similaridade total é calculada. Alinhamento local – Alinha regiões de alta similaridade entre duas sequências; – Muito usada na busca em banco de dados; – Útil na detecção de regiões repetitivas; – Útil na detecção de domínios conservados. Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento

Alinhamento global e a importância do GAP 1 AGGATTGGAATGCTCAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG ||||||| | | || | 1 AGGATTGGAATGCTACAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG Algorithm: GAP (Needleman & Wunsch) Produces an end-to-end alignment Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento 67 68

Alinhamento global e a importância do GAP 1 AGGATTGGAATGCTCAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG ||||||| | | || | 1 AGGATTGGAATGCTACAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG Algorithm: GAP (Needleman & Wunsch) Produces an end-to-end alignment Instituto Química - UFRJ|| Alinhamentodedesequencias sequências Tópicos emde Bioinformática || Alinhamento 67 68

Alinhamento global e a importância do GAP 1 AGGATTGGAATGCTCAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG ||||||| | | || | 1 AGGATTGGAATGCTACAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG 1 AGGATTGGAATGCT. CAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG |||||||||||||||||||||||||||||||||| 1 AGGATTGGAATGCTACAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG 67 68 O alinhamento fica muito melhor com a introdução de um Algorithm: GAP (Needleman & Wunsch) Produces an end-to-end alignment Instituto de Química - UFRJ|| Alinhamento de sequências

Alinhamento Local 1 AGGATTGGAATGCTCAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG. . . ||||||| || | || 1 AGGATTGGAATGCTAGGCTTGATTGCCTACCTGTAGCCACATCAGAAGCACTAAAGCGTCAGCGAGACCG Duas sequências podem compartilhar várias regiões similares. Observem os blocos de cores iguais. Instituto de Química - UFRJ|| Alinhamento de sequências 67 70
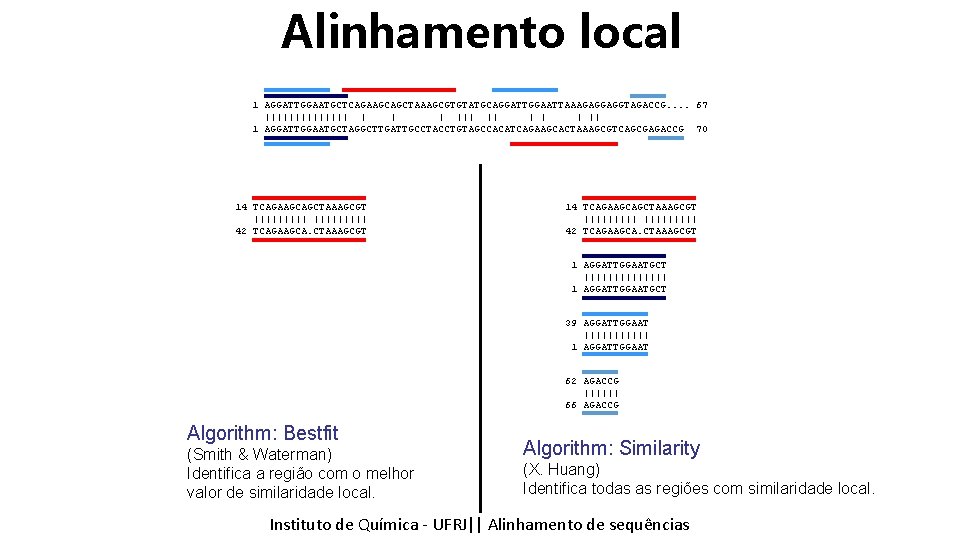
Alinhamento local 1 AGGATTGGAATGCTCAGAAGCAGCTAAAGCGTGTATGCAGGATTGGAATTAAAGAGGAGGTAGACCG. . 67 ||||||| || | || 1 AGGATTGGAATGCTAGGCTTGATTGCCTACCTGTAGCCACATCAGAAGCACTAAAGCGTCAGCGAGACCG 70 14 TCAGAAGCAGCTAAAGCGT ||||||||| 42 TCAGAAGCA. CTAAAGCGT 1 AGGATTGGAATGCT ||||||| 1 AGGATTGGAATGCT 39 AGGATTGGAAT |||||| 1 AGGATTGGAAT 62 AGACCG |||||| 66 AGACCG Algorithm: Bestfit (Smith & Waterman) Identifica a região com o melhor valor de similaridade local. Algorithm: Similarity (X. Huang) Identifica todas as regiões com similaridade local. Instituto de Química - UFRJ|| Alinhamento de sequências

Onde usamos alinhamento de sequências? ? ? ? Instituto de Química - UFRJ|| Alinhamento de sequências
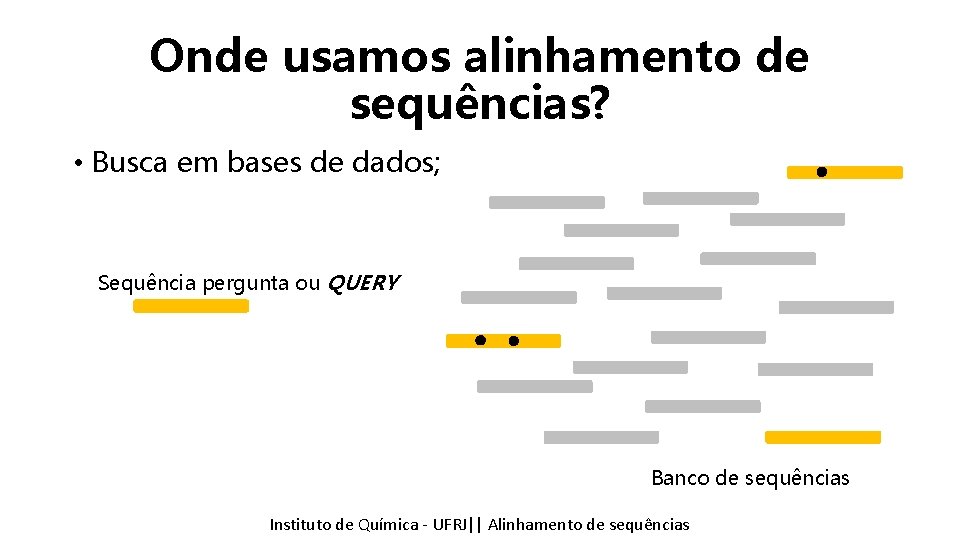
Onde usamos alinhamento de sequências? • Busca em bases de dados; Sequência pergunta ou QUERY Banco de sequências Instituto de Química - UFRJ|| Alinhamento de sequências
Onde usamos alinhamento de sequências? • Busca em bases de dados; • Estudos evolutivos; • Taxonomia de espécies; Instituto de Química - UFRJ|| Alinhamento de sequências
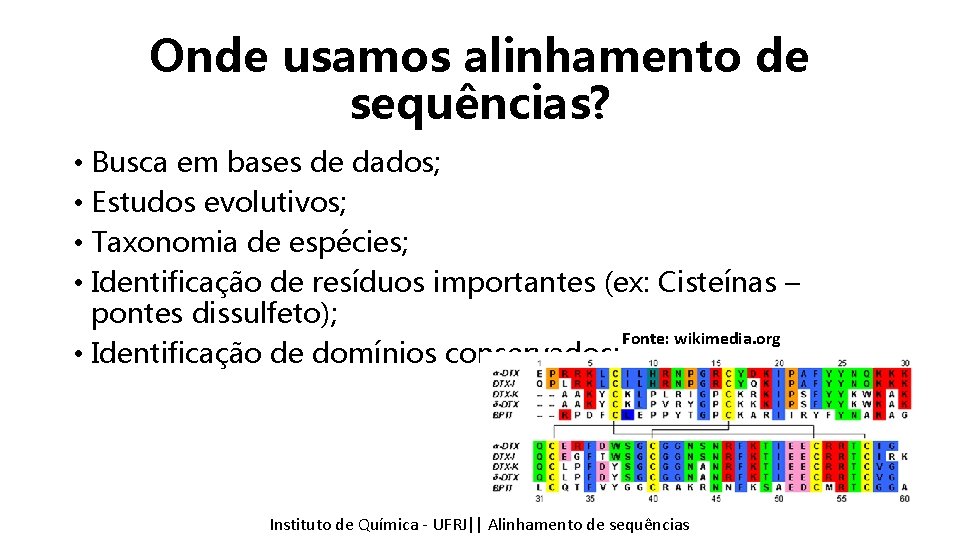
Onde usamos alinhamento de sequências? • Busca em bases de dados; • Estudos evolutivos; • Taxonomia de espécies; • Identificação de resíduos importantes (ex: Cisteínas – pontes dissulfeto); Fonte: wikimedia. org • Identificação de domínios conservados; Instituto de Química - UFRJ|| Alinhamento de sequências
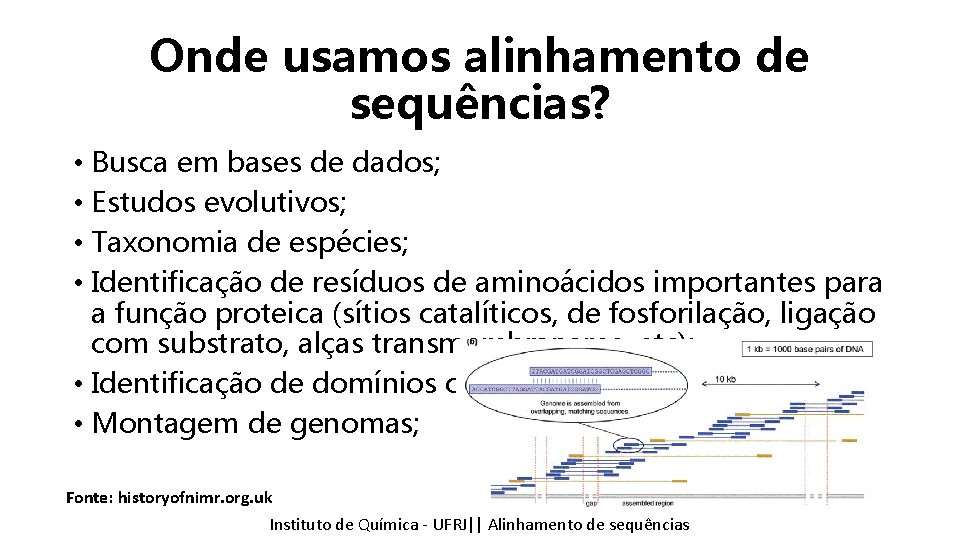
Onde usamos alinhamento de sequências? • Busca em bases de dados; • Estudos evolutivos; • Taxonomia de espécies; • Identificação de resíduos de aminoácidos importantes para a função proteica (sítios catalíticos, de fosforilação, ligação com substrato, alças transmembranares, etc); • Identificação de domínios conservados; • Montagem de genomas; Fonte: historyofnimr. org. uk Instituto de Química - UFRJ|| Alinhamento de sequências

Onde usamos alinhamento de sequências? • Busca em bases de dados; • Estudos evolutivos; • Taxonomia de espécies; • Identificação de resíduos de aminoácidos importantes para a função proteica (sítios catalíticos, de fosforilação, ligação com substrato, alças transmembranares, etc); • Identificação de domínios conservados; • Montagem de genomas; MAKCLGDEVPRY • Modelagem comparativa de proteínas. Instituto de Química - UFRJ|| Alinhamento de sequências Fonte: rcsb. org

Alguns softwares interessantes • Clustalw - Mais utilizado; • Praline - Leva em conta estrutura secundária da proteína e/ou presença de alças transmembranares; • T-coffee expresso – usa informação da estrutura terciária das proteínas; • MAFFT – Ótimo para um grande número de sequências; • Bowtie – montagem de genomas e transcriptomas; • BLAST – Busca por sequências em bancos de dados. Instituto de Química - UFRJ|| Alinhamento de sequências

Obrigado! Instituto de Química - UFRJ|| Alinhamento de sequências
- Slides: 63