Algorithmes doptimisation et danalyse des problmes multidimensionnels non

Algorithmes d’optimisation et d’analyse des problèmes multidimensionnels non linéaires en Biologie et Biophysique Soutenance de thèse Benjamin Parent Directeurs : Bernard Vandenbunder Jean-Pierre Richard 29 octobre 2007

Plan de la présentation 0. Introduction 1. Échantillonnage conformationnel 2. Modélisation en Biologie systémique 3. Conclusion

Introduction Modélisation moléculaire Biologie systémique Conclusion Objectifs de la thèse Appliquer les savoir-faire de l’Automatique à des problèmes issus de la Biologie et de la Biochimie dans la cellule, tout repose sur des interactions moléculaires… Étudier les interactions moléculaires À l’échelle des molécules individuelles Prédiction dans les cas « simples » Aide à l’interprétation des expériences Leur impact à l’échelle d’un module fonctionnel de la cellule 3/53
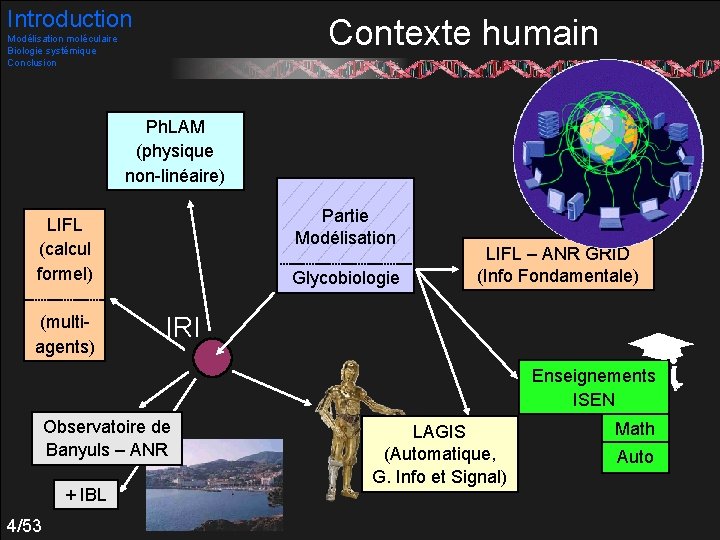
Introduction Contexte humain Modélisation moléculaire Biologie systémique Conclusion Ph. LAM (physique non-linéaire) Partie Modélisation LIFL (calcul formel) (multiagents) Glycobiologie LIFL – ANR GRID (Info Fondamentale) IRI Enseignements ISEN Observatoire de Banyuls – ANR + IBL 4/53 LAGIS (Automatique, G. Info et Signal) Math Auto

Plan de la présentation 0. Introduction 1. Échantillonnage conformationnel 2. Modélisation en Biologie systémique 3. Conclusion

Échantillonnage conformationnel Problématique et codage Algorithme génétique Hybridations Méta optimisation Parallélisation

Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage Vers une estimation des affinités entre cibles moléculaires (docking) Nécessité de décrire la flexibilité de chaque agent : exercice de prédiction de la géométrie des ligands des sites actifs (10 à 1000 atomes) 7/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage Stabilité donnée par les niveaux d’énergie Boltzmann : E estimée sur la base d’un champ de forces Hagler et al. [1974] Conformations adoptées en solution 8/53 = Minima de la fonction énergie
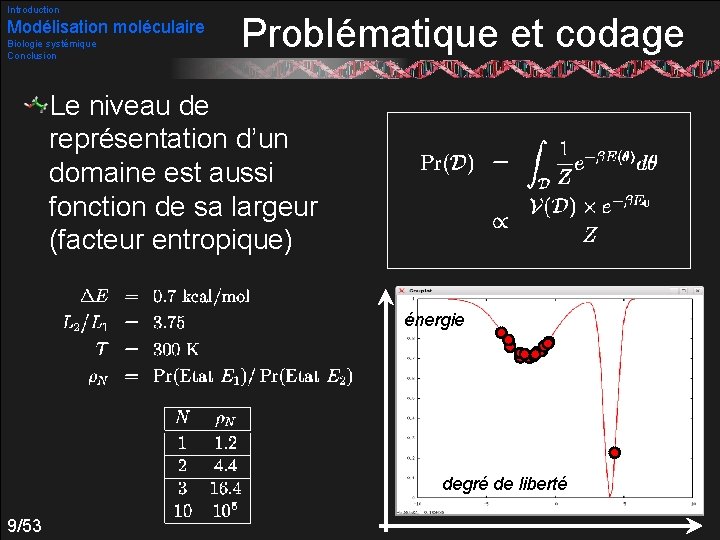
Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage Le niveau de représentation d’un domaine est aussi fonction de sa largeur (facteur entropique) énergie degré de liberté 9/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage La flexibilité des molécules repose essentiellement sur la libre rotation autour des liaisons inter atomiques 10/53
11/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage Que doit faire l’algorithme ? Explorer l’espace des géométries pour identifier les conformations stables Décrire les niveaux de peuplement des minima pertinents Idéal : reconstruire la densité de probabilité sur l’espace de phases Fichier moléculaire initial Algorithme Différentes conformations moléculaires Comparaisons possibles avec les expériences 12/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage Validation des résultats avec des molécules dont la structure est connue expérimentalement Filippine Tryp. ZIP 13/53 Cyclo- mini dextrine -turn Tryp. Cage Domaine WW de PIN

Introduction Modélisation moléculaire Biologie systémique Conclusion Problématique et codage Problème mathématique de minimisation de fonction Particularités : Très grandes dimensions (1… 200 degrés de liberté) Fortement multimodal (donc non linéaire) Recherche de tous les minima utiles Littérature 14/53 Molécules de petites tailles Vengadesan [2003] Grandes molécules, modèle simplifié Dynamique moléculaire Roitberg [2007]

Échantillonnage conformationnel Problématique et codage Algorithme génétique Hybridations Méta optimisation Parallélisation
![Introduction Modélisation moléculaire Biologie systémique Conclusion Algorithme génétiques Choix d’une stratégie : Holland [1975] Introduction Modélisation moléculaire Biologie systémique Conclusion Algorithme génétiques Choix d’une stratégie : Holland [1975]](http://slidetodoc.com/presentation_image_h2/80b7e2a605427cef5b14113ea7c064e3/image-16.jpg)
Introduction Modélisation moléculaire Biologie systémique Conclusion Algorithme génétiques Choix d’une stratégie : Holland [1975] les algorithmes génétiques (AG) + forte exploration de l’espace + population de solutions + concept d’héritage + modularité et adaptabilité – consommateurs de ressources – visitent les régions aberrantes – stochastiques (mauvaise reproductibilité) 16/53
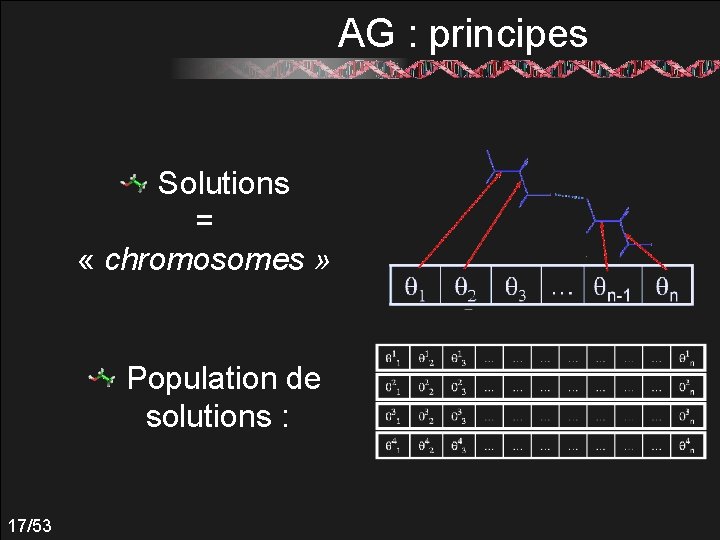
AG : principes Solutions = « chromosomes » Population de solutions : 17/53

AG : principes Évolution : opérateurs de croisement parent 1 : q 1 q 2 … qi qi+1 … qn fils 1 : q 1 q 2 … qi q ’i+1 … q ’n parent 2 : q ’ 1 q ’ 2 … q ’i+1 … q ’n fils 2 : q ’ 1 q ’ 2 … q ’i qi+1 … qn mutant : q 1 q 2 … q ’i qi+1 … qn … et de mutation muté : 18/53 q 1 q 2 … qi qi+1 … qn
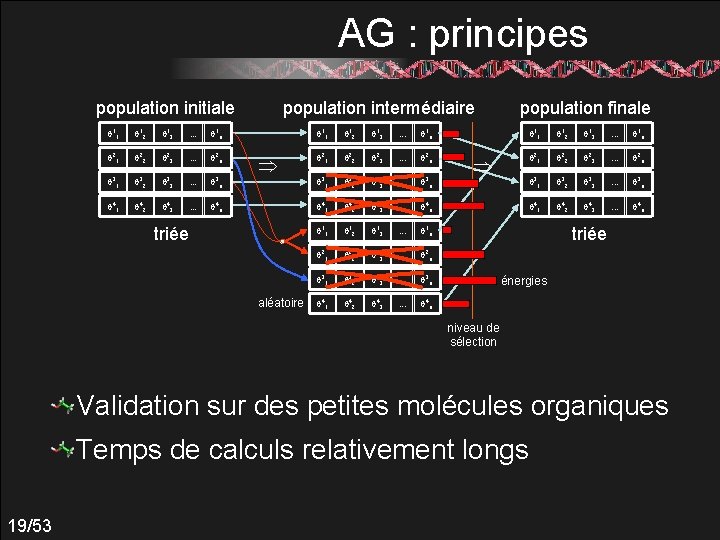
AG : principes population initiale population intermédiaire population finale q 11 q 12 q 13 . . . q 1 n q 21 q 22 q 23 . . . q 2 n q 31 q 32 q 33 . . . q 3 n q 41 q 42 q 43 . . . q 4 n q 11 q 12 q 13 . . . q 1 n q 21 q 22 q 23 . . . q 2 n q 31 q 32 q 33 . . . q 3 n q 41 q 42 q 43 . . . q 4 n triée aléatoire triée énergies niveau de sélection Validation sur des petites molécules organiques Temps de calculs relativement longs 19/53

Échantillonnage conformationnel Problématique et codage Algorithme génétique Hybridations Méta optimisation Parallélisation

Introduction Modélisation moléculaire Biologie systémique Conclusion Hybridations Algorithmes génétiques Relativement lents Ne tirent pas parti de la physique du problème Hybridation par des heuristiques complémentaires : Monte Carlo Fragmentation Recherche taboue Distributions de probabilité biaisées Mutations Dirigées 21/53
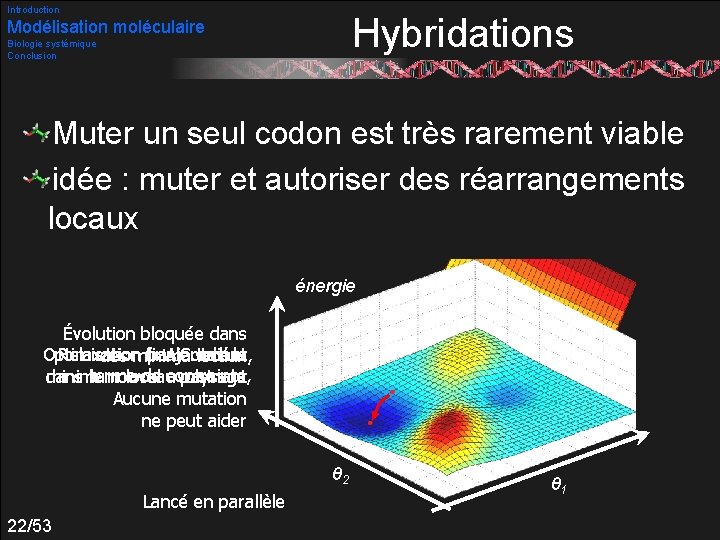
Introduction Hybridations Modélisation moléculaire Biologie systémique Conclusion Muter un seul codon est très rarement viable idée : muter et autoriser des réarrangements locaux énergie Évolution bloquée dans d’un Relaxation finale vers le Optimisation par. Ajout Gradient des minima locaux, terme de contrainte, minimum local avoisinant dans le nouveau paysage Aucune mutation ne peut aider θ 2 Lancé en parallèle 22/53 θ 1

Introduction Modélisation moléculaire Biologie systémique Conclusion Hybridations Jeux de tests : Par défaut, toutes les stratégies activées Puis, tour à tour, désactivation d’une heuristique : Sans mutation dirigée Sans tabou Distributions uniformes Distributions minimisant les tensions locales Trois à quatre tests pour chaque 23/53
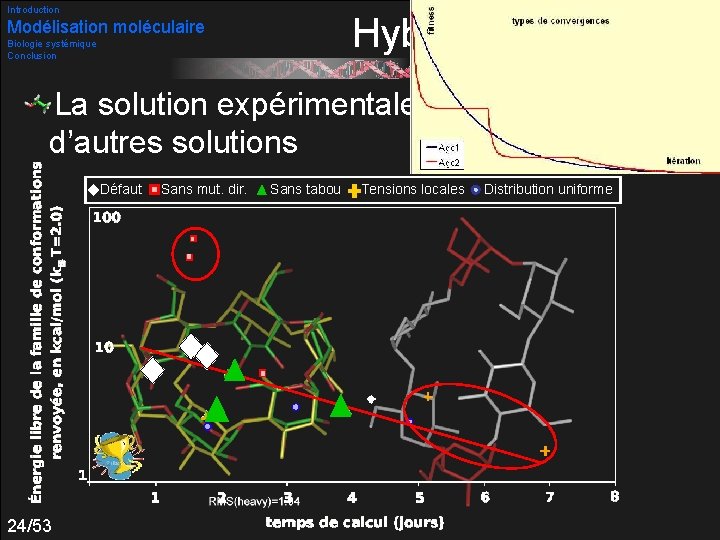
Introduction Hybridations Modélisation moléculaire Biologie systémique Conclusion La solution expérimentale est trouvée parmi d’autres solutions Défaut 24/53 Sans mut. dir. Sans tabou Tensions locales Distribution uniforme

Échantillonnage conformationnel Problématique et codage Algorithme génétique Hybridations Méta optimisation Parallélisation

Introduction Modélisation moléculaire Biologie systémique Conclusion Méta optimisation Les performances des AG dépendent (fortement) des « hyper paramètres » de contrôle : Gestion de la population Gestion de l’évolution Taille de population Taux de croisement Nombre de processus parallèles Taux de mutation Taux de migration Croisements à un et deux points Gestion de la convergence Pression de sélection Fréquence des apocalypses Élitisme Condition globale d’arrêt ge maximal Limite de dissimilitude 26/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Pression de sélection Élitisme ge maximal Limite de dissimilitude nouvellegénérationtemporaire 27/53 Méta optimisation

Introduction Méta optimisation Modélisation moléculaire Biologie systémique Conclusion Gestion de la population Taille Gestion de population de l’évolution Nombre processus parallèles Taux Pression dede croisement de sélection Taux de migration Taux de mutation Élitisme Gestion de la convergence A. G. p 1 p 2 p 3 p 4 Croisements un et deux points ge maximalàdes Fréquence apocalypses Limite de dissimilitude Condition globale d’arrêt p 5 p 6 pn Que faire avec ces paramètres ? 28/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Méta optimisation Comment définir une stratégie optimale ? Comment comparer deux exécutions ? Dans un contexte stochastique ? La « meilleure » stratégie dépend-elle de la molécule traitée ? Question ouverte : comment connaître a priori des hyper paramètres satisfaisants ? 29/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Méta optimisation Problème d’optimisation classique Évaluation de la qualité d’un échantillonnage : Abordé par « méta » -algorithme génétique (µ-AG) 30/53
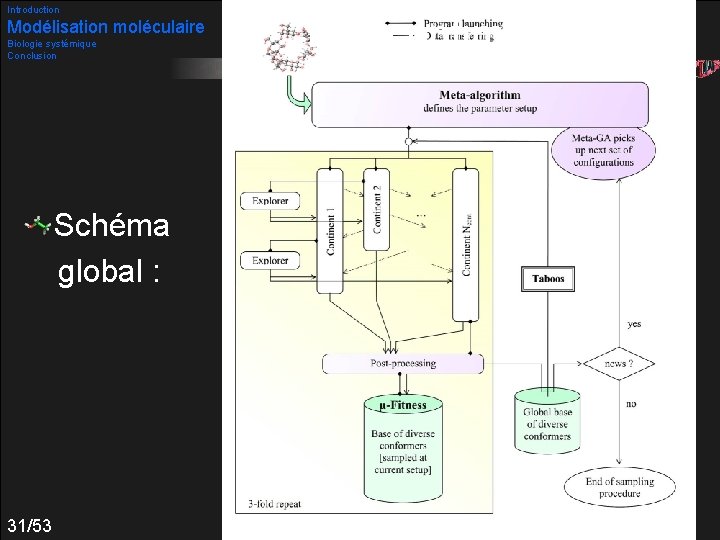
Introduction Modélisation moléculaire Biologie systémique Conclusion Schéma global : 31/53 Méta AG paramétré optimisation
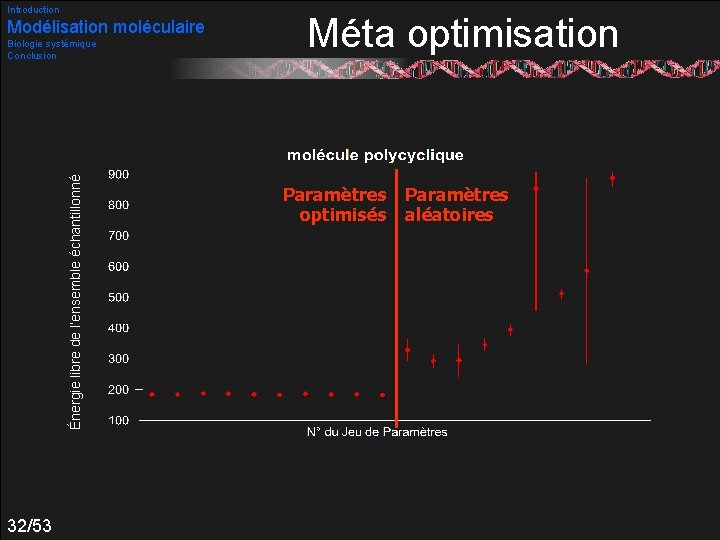
Introduction Modélisation moléculaire Énergie libre de l’ensemble échantillonné Biologie systémique Conclusion 32/53 Méta optimisation Paramètres optimisés Paramètres aléatoires

Introduction Modélisation moléculaire Biologie systémique Conclusion Méta optimisation Validations (résumé) : Capacité exploratrice des AG Stratégie de méta optimisation des hyper paramètres Hybridation avec heuristiques complémentaires Parent [2007 a] Amélioration des temps de calculs Long pour les tests du méta AG Toujours prohibitif pour les plus grandes molécules 33/53

Échantillonnage conformationnel Problématique et codage Algorithme génétique Hybridations Méta optimisation Parallélisation

Introduction Modélisation moléculaire Biologie systémique Conclusion Parallélisation Projet ANR Docking@grid avec l’équipe OPAC du LIFL (Pr. Talbi) http: //dockinggrid. gforge. inria. fr/index. html Grid 5000 : environnement multiprocesseur Généralisation des îles : Multiplier les îles pas de sens Indépendance totale bénéfice de l’architecture grille ? Pande [2003] Utilisation des solutions précédemment échantillonnées 35/53
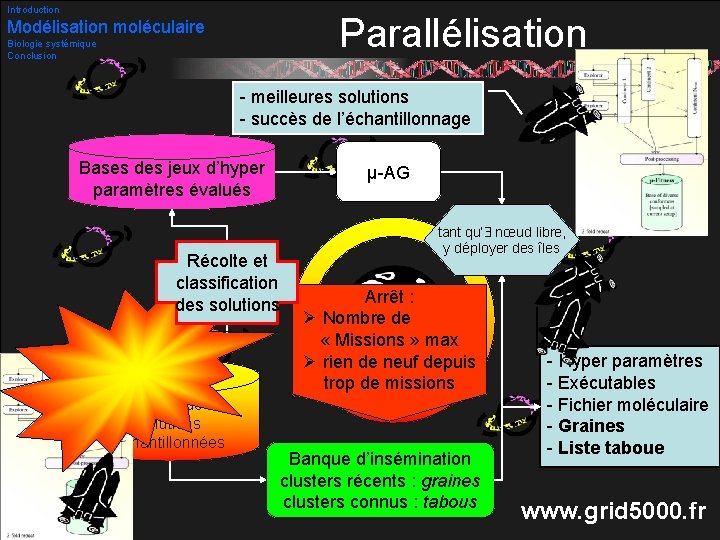
Introduction Parallélisation Modélisation moléculaire Biologie systémique Conclusion - meilleures solutions - succès de l’échantillonnage Bases des jeux d’hyper paramètres évalués Récolte et classification des solutions Bases de solutions échantillonnées 36/53 µ-AG tant qu’ nœud libre, y déployer des îles Arrêt : Ø Nombre de « Missions » max Ø rien de neuf depuis trop de missions Banque d’insémination clusters récents : graines clusters connus : tabous - Hyper paramètres - Exécutables - Fichier moléculaire - Graines - Liste taboue www. grid 5000. fr

Introduction Modélisation moléculaire Biologie systémique Conclusion Parallélisation Stratégie : surveiller la (re)visite de régions de solutions Classification : par énergies autour des plus stables (paramètre de taille Dmax) Panspermie : insémination des planètes par Des « graines » attractrices (régions plus récentes que Nintens missions) Des tabous répulsifs (déjà intensifiés) Régler Dmax et Nintens est un problème délicat ! 37/53
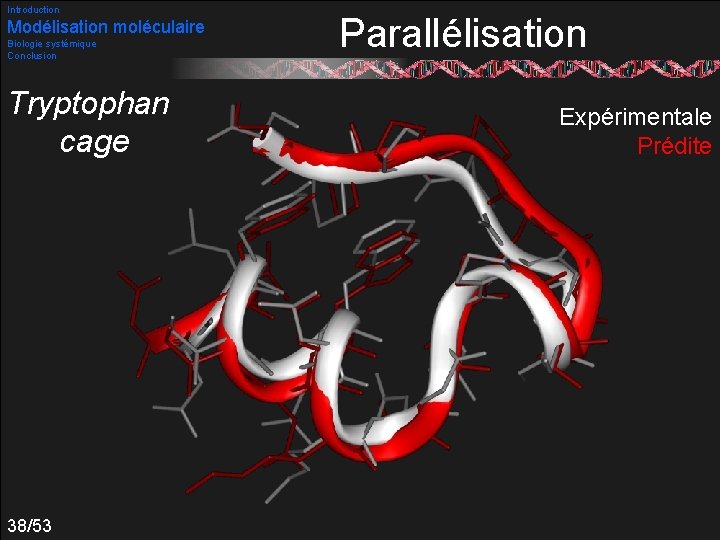
Introduction Modélisation moléculaire Biologie systémique Conclusion Tryptophan cage 38/53 Parallélisation Expérimentale Prédite
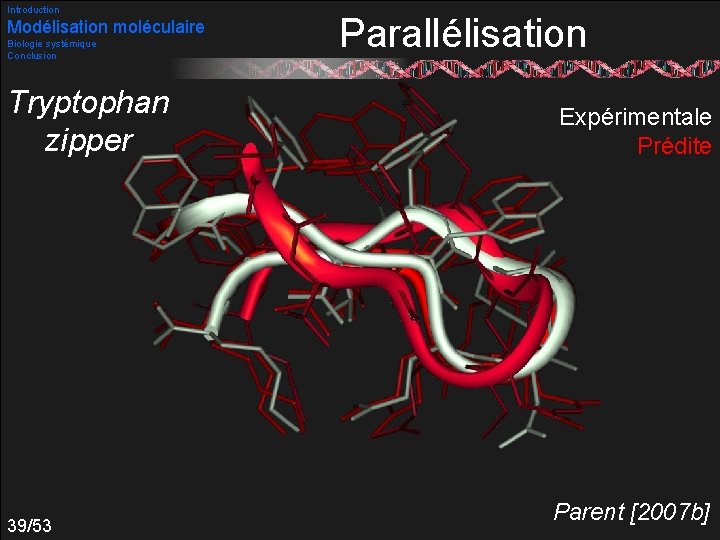
Introduction Modélisation moléculaire Biologie systémique Conclusion Tryptophan zipper 39/53 Parallélisation Expérimentale Prédite Parent [2007 b]

Introduction Modélisation moléculaire Biologie systémique Conclusions et perspectives Acquis : Suite d’algorithmes efficaces et adaptatifs Stratégies d’hybridation Premiers déploiements parallèles Vers du docking (résultats non-présentés) : Outil de positionnement relatif de deux molécules Stratégie de criblage Bonachéra [2006] Perspectives : Déploiements massivement parallèles Développement de nouvelles stratégies Meilleure caractérisation des conformations 40/53 Algorithme de docking

Plan de la présentation 0. Introduction 1. Échantillonnage conformationnel 2. Modélisation en Biologie systémique 3. Conclusion

Introduction Modélisation moléculaire Problématique Biologie systémique Conclusion La forme des interactions a-t-elle un impact sur les dynamiques ? À l’échelle de la cellule : impossible de décrire L’ensemble des événements moléculaires L’ensembles de acteurs Recours à un modèle : les concentrations Continues Déterministes Dimension finie 42/53 (solutions d’équations différentielles ordinaires)
Introduction Modélisation moléculaire Biologie systémique Rythmes circadiens Conclusion On observe : Des oscillations qui perdurent en conditions d’éclairement constant, avec période 24 h Une compensation en température (robustesse de la période) La possibilité de réinitialiser le système 43/53
Introduction Modélisation moléculaire Biologie systémique Réseaux de régulation Conclusion protéine : p ADN promo teur gène : ABC prot : abc Nakajima [2005] 44/53
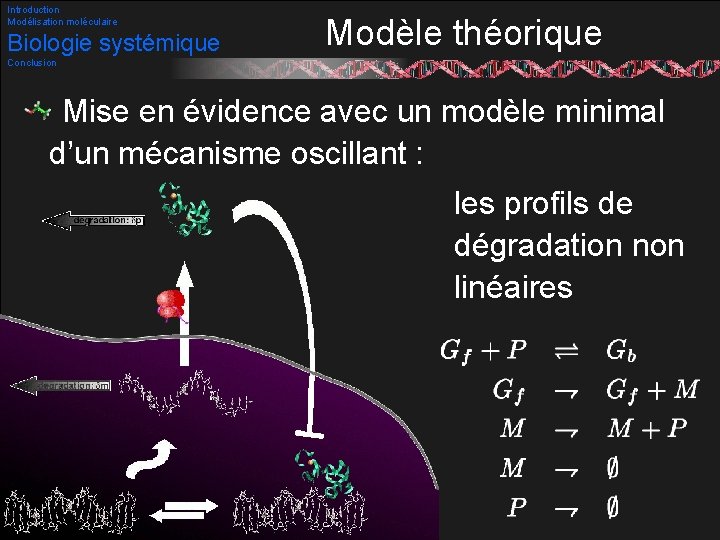
Introduction Modélisation moléculaire Biologie systémique Modèle théorique Conclusion Mise en évidence avec un modèle minimal d’un mécanisme oscillant : les profils de dégradation non linéaires 45/53

Introduction Modélisation moléculaire Biologie systémique Modèle théorique Conclusion But : déstabiliser le système 46/53
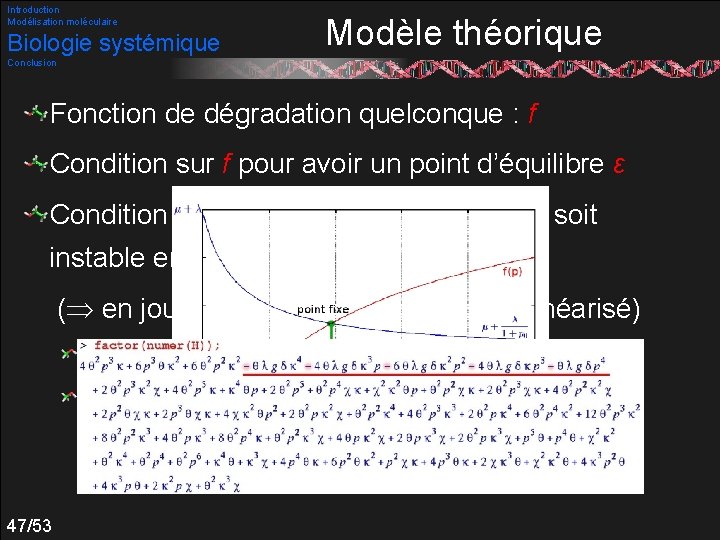
Introduction Modélisation moléculaire Biologie systémique Modèle théorique Conclusion Fonction de dégradation quelconque : f Condition sur f pour avoir un point d’équilibre ε Condition sur les paramètres pour que ε soit instable entouré d’un cycle limite ( en jouant sur les pôles du modèle linéarisé) On montre que f linéaire n’est pas suffisante Qu’il est nécessaire que la dégradation soit saturée 47/53

Introduction Modélisation moléculaire Biologie systémique Exemple : Michaëlis- Menten Conclusion f(p)=a. p/(b+p) Beaucoup utilisée Il est possible de remonter aux domaines de paramètres générant des oscillations : 48/53
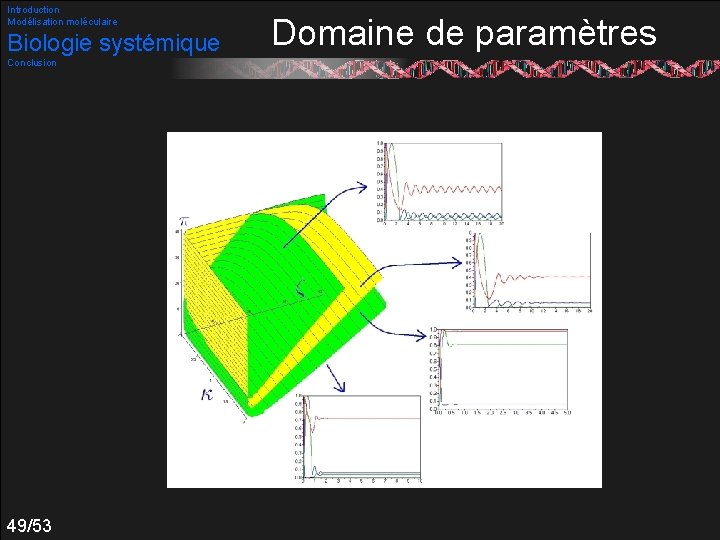
Introduction Modélisation moléculaire Biologie systémique Conclusion 49/53 Domaine de paramètres
Introduction Modélisation moléculaire Biologie systémique Conclusion, perspectives Conclusion Acquis : mise en évidence d’un mécanisme déstabilisant par une approche purement formelle Perspectives : Confronter des valeurs expérimentales avec les domaines trouvés Évaluer la robustesse du système par rapport aux variations de température Autres mécanismes déstabilisants : diffusion ( propagation) 50/53

Plan de la présentation 0. Introduction 1. Échantillonnage conformationnel 2. Modélisation en Biologie systémique 3. Conclusion

Introduction Modélisation moléculaire Biologie systémique Conclusion Dans la description des interactions, il existe un fossé entre les événements moléculaires individuels et la dynamique des modules fonctionnels Le rôle de l’interdisciplinaire est primordial 52/53

Introduction Modélisation moléculaire Biologie systémique Conclusion Articles : C I i Bonachéra F. , Parent B. , Horvath D. (2006) Journal of Chemicalrc Models e Parent B. , Kökosy A. , Horvath D. (2007) Soft Computing m Tantar A. -A. , Melab N. , Talbi E. -G. , Parent B. , Horvath D. (2007) Future Generation Computer Systems i A. , Wieruszeski J. -M. , c Hanoulle X. , Melchior A. , Sibille N. , Parent B. , Denys r e Horvath D. , Allain F. , Lippens G. , Landrieu I. (2007) Journal of Biological m Chemistry Conférences : E ci r e R m D. (2006) Gordon Research Conference, Parent B. , Lippens G. , Horvath Suisse Parent B. , Tantar A. -A. , Melab N. , Talbi E. -G. , Horvath D. (2007) Congress ci on Evolutionary Computation, Singapour r e m Morant P. -E. , Vandermoere C. , Thommen Q. , Parent B. , Lemaire F. , Corellou F. , Schwartz C. , Bouget F. -Y. , Lefranc M. (2007) Rencontres du Non. Linéaire, Paris 53/53 M
- Slides: 53