AFRIKAI HARCSA GENOM PROJECT Kovcs Balzs 1 Barta

AFRIKAI HARCSA GENOM PROJECT Kovács Balázs 1, Barta Endre 2, Pongor Lőrinc 3, Uri Csilla 1, Keszte Szilvia 1, Patócs Attila 3, Müller Tamás 1, Orbán László 4, Urbányi Béla 1 1 Szent István Egyetem, Mezőgazdaság- és Környezettudományi Kar, Akvakultúra és Környezetbiztonsági Intézet, Halgazdálkodási Tanszék, Gödöllő 2 NAIK Mezőgazdasági Biotechnológiai Kutatóintézet, Mezőgazdasági Genomika és Bioinformatika Csoport, Gödöllő 3 MTA-SE Molekuláris Medicina Kutatócsoport, Semmelweis Egyetem, Budapest 4 Reproductive Genomics Group, Temasek Life Sciences Laboratory, Singapore
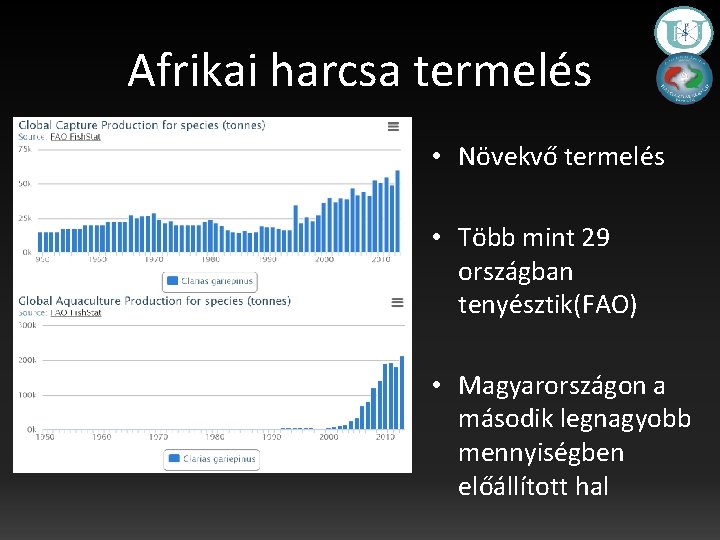
Afrikai harcsa termelés • Növekvő termelés • Több mint 29 országban tenyésztik(FAO) • Magyarországon a második legnagyobb mennyiségben előállított hal
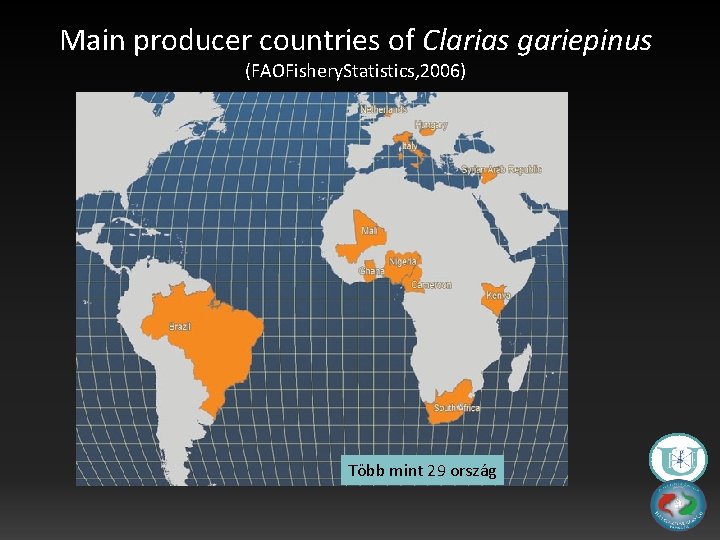
Main producer countries of Clarias gariepinus (FAOFishery. Statistics, 2006) Több mint 29 ország
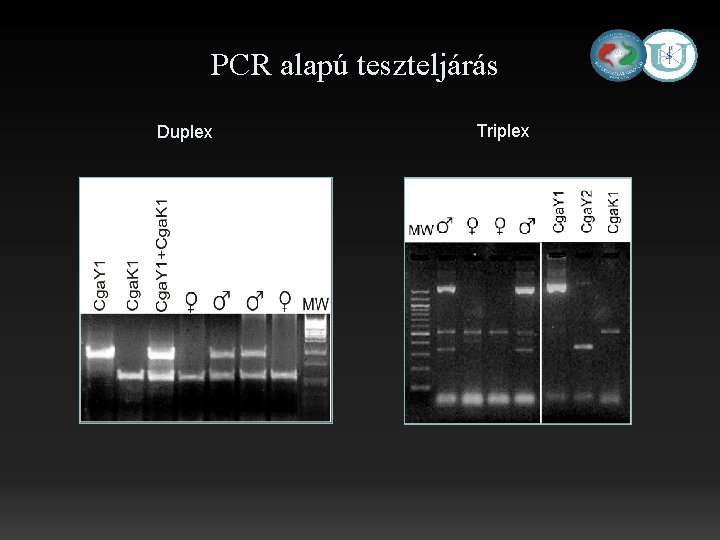
PCR alapú teszteljárás Duplex Triplex
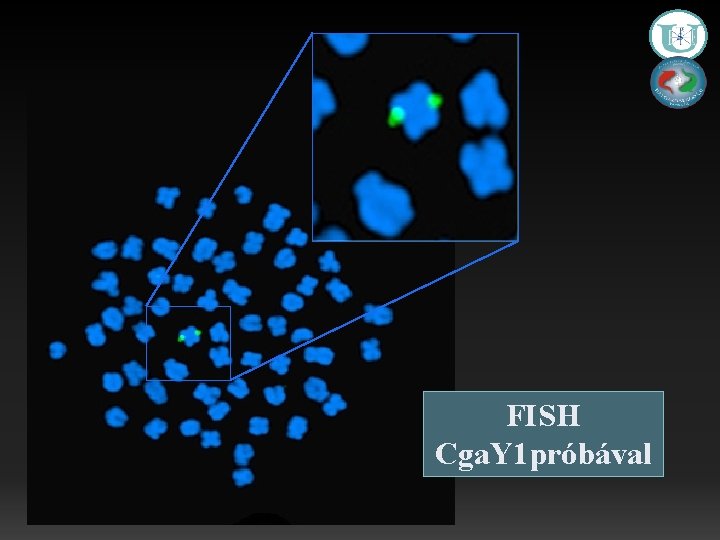
FISH Cga. Y 1 próbával
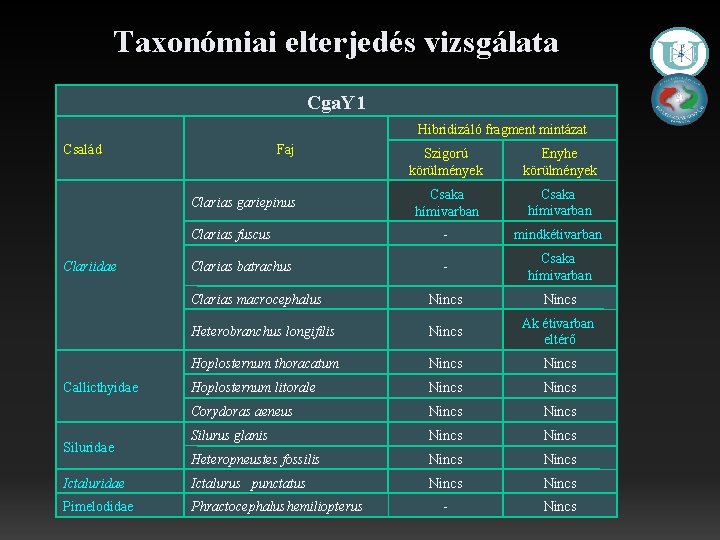
Taxonómiai elterjedés vizsgálata Cga. Y 1 Hibridizáló fragment mintázat Család Faj Szigorú körülmények Enyhe körülmények Csaka hímivarban Clarias fuscus - mindkétivarban Clarias batrachus - Csaka hímivarban Clarias macrocephalus Nincs Heterobranchus longifilis Nincs Ak étivarban eltérő Hoplosternum thoracatum Nincs Hoplosternum litorale Nincs Corydoras aeneus Nincs Silurus glanis L Nincs Heteropneustes fossilis Nincs Ictaluridae Ictaulurus Ictalurus punctatus Nincs Pimelodidae Phractocephalus hemiliopterus Phractocephalushemiliopterus - Nincs Clarias gariepinus Clariidae Callichthyidae Callicthyidae Siluridae
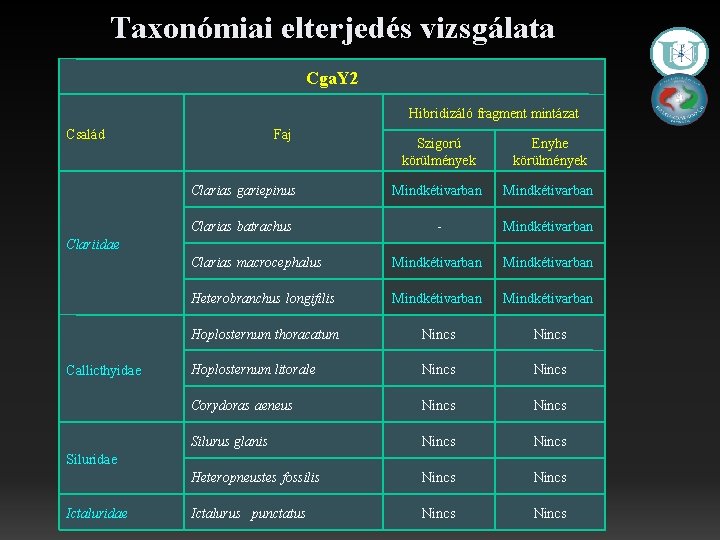
Taxonómiai elterjedés vizsgálata Cga. Y 2 Hibridizáló fragment mintázat Család Faj Szigorú körülmények Enyhe körülmények Clarias gariepinus Mindkétivarban Clarias batrachus - Mindkétivarban Clarias macrocephalus Mindkétivarban Heterobranchus longifilis Mindkétivarban Hoplosternum thoracatum Nincs Hoplosternum litorale Nincs Corydoras aeneus Nincs Silurus glanis L Nincs Heteropneustes fossilis Nincs Ictaulurus punctatus Ictalurus Nincs Clariidae Callichthyidae Callicthyidae Siluridae Ictaluridae
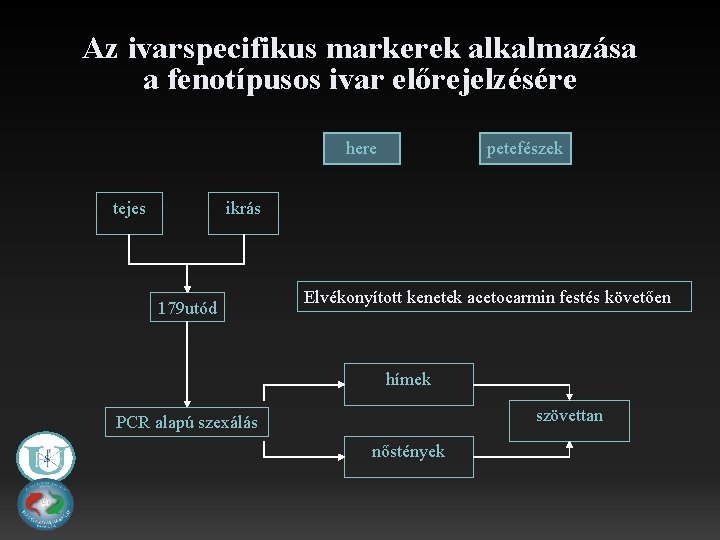
Az ivarspecifikus markerek alkalmazása a fenotípusos ivar előrejelzésére here tejes petefészek ikrás 179 utód Elvékonyított kenetek acetocarmin festés követően hímek szövettan PCR alapú szexálás nőstények

Genom információk • Egy egyed (hím) • 2 n=56 (Okonkwoand Obiakor; 2010) • C-érték: 1. 20 pg (Animal Genome Size Database) • Számított genom méret: 1173 Mb
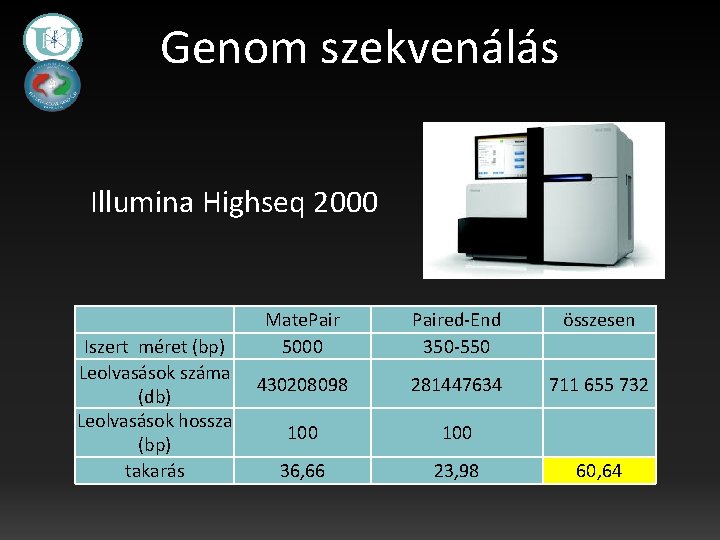
Genom szekvenálás Illumina Highseq 2000 Iszert méret (bp) Leolvasások száma (db) Leolvasások hossza (bp) takarás Mate. Pair 5000 Paired-End 350 -550 összesen 430208098 281447634 711 655 732 100 36, 66 23, 98 60, 64

Adat feldolgozás • Nemzeti Információs Infrastruktúra Fejlesztési (NIIF) Program • Szekvencia minőség vizsgálat: Trimmomatic • Az adataok 89% - a használható • A szekvencia összeillesztése (De Novo Genome Assembly): – SOAPdenovo – Allpaths-lg – Minia
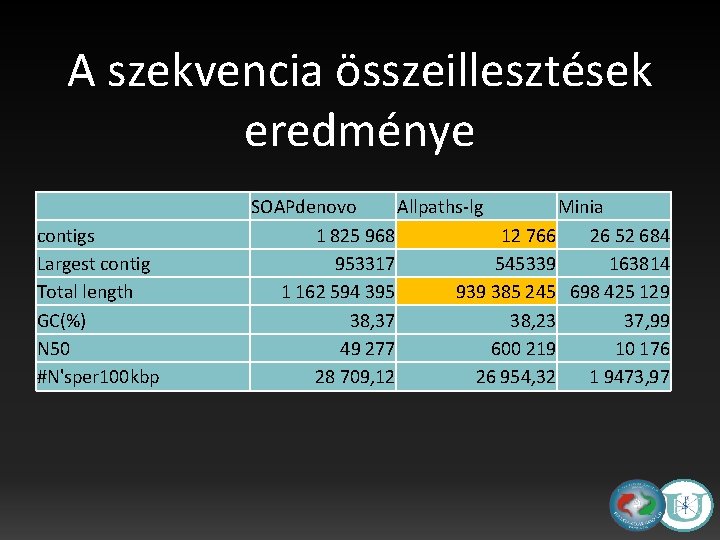
A szekvencia összeillesztések eredménye contigs Largest contig Total length GC(%) N 50 #N'sper 100 kbp SOAPdenovo Allpaths-lg Minia 1 825 968 12 766 26 52 684 953317 545339 163814 1 162 594 395 939 385 245 698 425 129 38, 37 38, 23 37, 99 49 277 600 219 10 176 28 709, 12 26 954, 32 1 9473, 97
Szekvencia Illesztés

Ivari markerek a szekvenciában • Mind két markert megtalálható – Cga. Y 1 6 Kb Contig – Cga. Y 2 44 kb contig

A mitokondriális DNS annotálása • 16 543 bp • 37 gén MITOS- szoftver Name t. RNAPhe 12 S r. RNA t. RNAVal 16 S r. RNA t. RNALeu ND 1 t. RNAIle t. RNAGln t. RNAMet ND 2 t. RNATrp t. RNAAla t. RNAAsn t. RNACys t. RNATyr COX 1 t. RNASer t. RNAAsp COX 2 t. RNALys Start 1 70 1022 1094 2768 2846 3823 3894 3964 4034 5079 5153 5223 5327 5405 5482 7027 7102 7189 7880 Stop 69 1021 1093 2769 2842 3811 3894 3964 4033 5071 5149 5221 5295 5393 5474 7017 7097 7174 7872 7953 Length 69 952 72 1676 75 966 72 71 70 1038 71 69 73 67 70 1536 71 73 684 74 Strand H H H H L L H L H H H Name ATP 8 ATP 6 COX 3 t. RNAGly ND 3 t. RNAArg NAD 4 L NAD 4 t. RNAHis t. RNASer t. RNALeu NAD 5 NAD 6 t. RNAGlu Cyt b t. RNAThr t. RNAPro Start 7955 8113 8796 9609 9682 10031 10100 10390 11771 11841 11909 11991 13808 14324 14394 15532 15603 Stop 8119 8793 9578 9681 10029 10099 10393 11763 11840 11906 11981 13796 14323 14392 15521 15604 15672 Length 165 681 783 73 348 69 294 1374 70 66 73 1806 516 69 1128 73 70 Strand H H H L L H H L
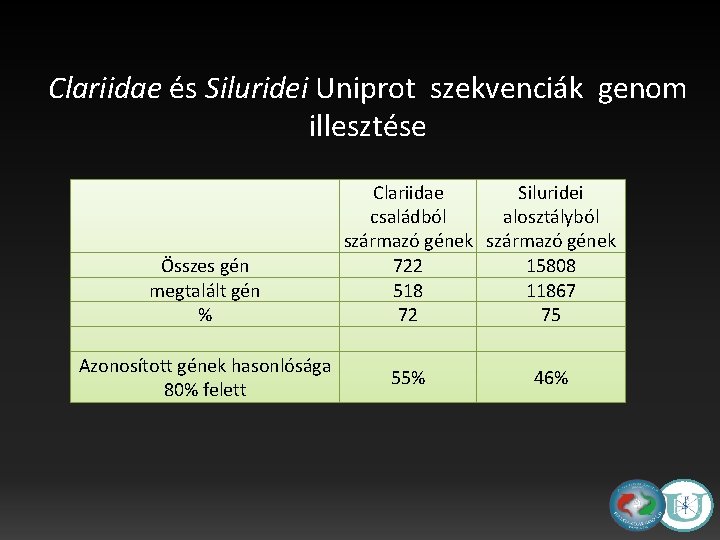
Clariidae és Siluridei Uniprot szekvenciák genom illesztése Összes gén megtalált gén % Azonosított gének hasonlósága 80% felett Clariidae Siluridei családból alosztályból származó gének 722 15808 518 11867 72 75 55% 46%

Összefoglalás • Mate. Pair és Paired-End genomi könyvtárak • Genom szekvencia adatok 60 x lefedettséggel • Mitokondriális genom (16 537 bp, 37 gén) • ~ 5460 db gén előzetes illesztése Folytatás • Újabb hosszú Inzert (large insert) genomi könyvtár és Teljes Transzkriptóma szekvenálás

Köszönetnyilvánítás A kutatást az OTKA 105393 és a Nemzeti Kíválóság Program 85265/2014/TUDPOL azonosító számú pályázata támogatja.
- Slides: 20