11 Vorlesung 7 Regelbasierte Modellierung Basissystem Analytisch Metabolisches

11. Vorlesung 7. Regelbasierte Modellierung Basissystem Analytisch Metabolisches System Vorlesung WS 06/07 Modellierung & Simulation Überblick
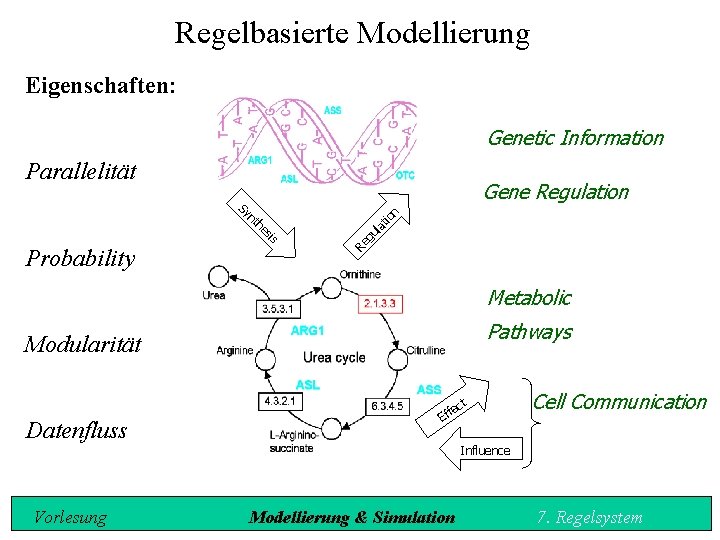
Regelbasierte Modellierung Eigenschaften: Genetic Information Parallelität Gene Regulation la gu Re sis he nt tio n Sy Probability Metabolic Pathways Modularität ct Datenfluss Vorlesung fe Ef Cell Communication Influence Modellierung & Simulation 7. Regelsystem

Das metabolische System Idee: Regelbasiertes System für die Formalisierung von: Biosyntheseprozessen, Proteinsyntheseprozessen, Metabolischen pathways sowie Zellkommunikationsprozessen. Grundlage ist eine universelle Regel: Spezifikation der Regelwahrscheinlichkeit (p). Vier weitere Komponenten = spezifische Metabolite. Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Metabolische Regel Sei Z die Menge aller möglichen Zellzustände. Eine metabolische Regel ist ein 5 Tupel (p, V, N, F, H), wobei p Î [0; 1] und V, N, F, H Í Z. p heißt Regelwahrscheinlichkeit, V ist eine Menge von Vorbedingungen, N ist eine Menge von Nachbedingungen, F ist die Menge der Förder-Substanzen (Förderer) und H ist die Menge der Hemm-Substanzen (Hemmer). Notation: Vorlesung Ist V, N, F oder H die leere Menge, so wird dies im weiteren durch Æ dargestellt. Modellierung & Simulation 7. Regelsystem

Basismodell ist ein diskretes Modell. Definition: Metabolisches Basissystem Ein metabolisches Basissystem ist ein Tripel G = (Z, R, z 0). Z bezeichnet die Menge aller möglichen Zellzustände, z 0 Î Z ist der Start Zell Zustand und R eine endliche Menge metabolischer Regeln. Arbeitsweise des metabolischen Basissystems. Grundidee: Vorlesung Eigenschaften der metabolischen Verarbeitung in das Modell integrieren. Modellierung & Simulation 7. Regelsystem

Definition: Aktivierung Sei G = (Z, R, z 0) ein metabolisches Basissystem. Die Regel r = (p, V, N, F, H) Î R heißt aktiviert im Zustand z Î Z, wenn gilt: x Î V x Î z und berechnen(r, z) > 0. AKT(z) = { r Î R : r ist aktiviert unter z } bezeichnet die Menge aller aktivierten Regeln im Zustand z. Gilt AKT(z) = Æ, dann terminiert G im Zustand z. r Î R ist aktiviert, wenn - V-Komponenten dieser Regel sind Elemente des aktuellen Zustandes und - Verrechnung der Einflussgemische hat eine modifizierte Regelwahrscheinlichkeit zur Folge, die größer als Null ist. Sie dient im zugehörigen Simulator einer booleschen Funktion random als Eingabe: true oder false, wobei im Fall true die Regel als ausführbar gilt ! Vorlesung Modellierung & Simulation 7. Regelsystem

Beispiel: Sei G = (Z, R, z 0) ein metabolisches System z 0 = {S, D} und R = {r 1, r 2} wobei r 1 = (0. 8, {S}, {H, S}, {D}, {L}) und r 2 = (0. 6, {D}, {X}, {E}, {D}). Unter der Konfiguration z 0 ist AKT(z 0) = {r 1}. Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Aktion Sei G = (Z, R, z 0) ein metabolisches Basissystem, z Î Z der aktuelle Zustand und r = (p, V, N, F, H) Î R eine aktivierte Regel. Die Aktion der im Zustand z aktivierten Regel r ist gegeben durch: z' = (z V) È N. Aktion der Regel r im Zustand z: Beispiel: z ® z' (symbolisch) Sei G wie oben. Die Aktion der aktivierten Regel r 1 führt zum Zustand z' = {H, S, D}. Vorlesung Modellierung & Simulation 7. Regelsystem

Nachfolgezustand: AKT(z) liefert eine potentielle Menge von Nachfolgezuständen ( (AKT(z)). Definition: Nachfolgezustand - Einschritt-Ableitung Sei G = (Z, R, z 0) ein metabolisches System. Sei z Î Z der aktuelle Zustand und T Í AKT(z) mit AKT(z) ¹ Æ. Die 'quasi' gleichzeitige Aktion der Regelmenge T führt zum Nachfolgezustand z' und heißt Einschritt Ableitung, in Symbolen z T z', wenn gilt: z' = (z VT) È NT, wobei VT = { m : $ r = (p, V, N, F, H) Î T m Î V } und NT = { m : $ r = (p, V, N, F, H) Î T m Î N }. Wir sagen: z wird mittels der Aktion T nach z' überführt. ABL(z) = { z' : $ TÍAKT(z) z ÞT z' } ist die Menge aller Nachfolgezustände aus z.

Beispiel: Sei G = (Z, R, z 0) ein metabolisches System mit z 0 = {B, C, E} und R = {r 1, r 2, r 3} mit r 1 = (0. 9, {B}, {S, B}, {C}, Æ), r 2 = (0. 3, {C}, {F, C}, {E}, Æ) und r 3 = (0. 3, {C, F}, {B, C}, {E}, Æ). AKT(z 0) = {r 1, r 2} ist die Menge der unter z 0 aktivierten Regeln. Aktion der Regel r 1 {B, C, E, S}. Im Zustand z 0 gibt es verschiedene Einschritt Ableitungen: {B, C, E, S} (Aktion von r 1), {B, C, E, F} (Aktion von r 2), {B, C, E, S, F} (Aktion von r 1 und r 2) und {B, C, E} (leere Aktion). Vorlesung Modellierung & Simulation 7. Regelsystem

Ableitung = Kaskade von Nachfolgezuständen. Definition: Ableitung Sei G = (Z, R, z 0) ein beliebiges metabolisches System. Eine Folge von Zuständen z 1, . . . , zn+1 heißt Ableitung von z 1 nach zn+1 mittels der Aktion T 1, . . . , Tn, wenn gilt: i=1, . . . , n zi ÞTi zi+1. Ferner ist die n Schritt Ableitung z Ti z' definiert, in Worten z ist in n Schritten nach z' ableitbar, wenn gilt: Es gibt Zustände z 1, . . . , zn+1 und Aktionen T 1, . . . , Tn, so dass z = z 1, z' = zn+1 und z 1 bis zn+1 ist eine Ableitung mittels der Aktionen T 1, . . . , Tn. Ferner ist z z', in Worten z ist ableitbar nach z', wenn es ein n gibt, so dass z Tn z' gilt. Vorlesung Modellierung & Simulation 7. Regelsystem

Beispiel: G wie bereits festgelegt. Dann ist die folgende Kaskade eine mögliche Ableitung: {B, C, E} ÞT {B, C, E, S} ÞT' {B, C, E, S, F} ÞT'' {B, C, E, S, F}. . . mit T = {r 1}, T' = {r 1, r 2} und T'' = {r 2, r 3}. Aktionswahrscheinlichkeit δ(p). Aktiviert ein Metabolitgemisch m eine Regel r = (p, V, N, F, H), so handelt es sich um das unabhängige Ereignis "r tritt bei m in Aktion" mit der Wahrscheinlichkeit δ(p). Vorlesung Modellierung & Simulation 7. Regelsystem

Wahrscheinlichkeit einer Ableitung Zunächst die Wahrscheinlichkeit der Einschritt Ableitung des Zellzustandes z in den Zellzustand z' ermitteln: P(z'|z). Sei z Î Z. Es werden alle Paare (m, r) mit mÍz und rÎAKT(z) (d. h. m aktiviert r) betrachtet. Seien (m 1, r 1), . . . , (mk, rk) diese Paare mit k Î N. Vorlesung Modellierung & Simulation 7. Regelsystem

Wahrscheinlichkeit einer Ableitung Ein jedes Wort w Î {L, R}k bezeichnet eine Menge von Ereignissen, die einen Generationswechsel beschreiben. Sei w = a 1 a 2. . ak, dann entspricht w dem Ereignis: für i = 1, . . . , k, ri tritt in Aktion bei Nachricht mi, falls ai = L und ri tritt nicht in Aktion bei Nachricht mi, falls ai = R. Vorlesung Modellierung & Simulation 7. Regelsystem

Dies sind unabhängige Ereignisse: P(w) : = Pi=1, . . . , k qi , wobei δ(pi), falls ai = L 1 - δ(pi), falls ai = R qi : = Jedes dieser Ereignisse w legt eine Ausgabenachricht α(w) fest: α(a 1. . ak) = { N : $ i Î {1, . . . , k} ai = L und ri = (p, V, N, F, H) }. D. h. : P(z'|z) = Sα(w)=z' P(w). Vorlesung Modellierung & Simulation 7. Regelsystem
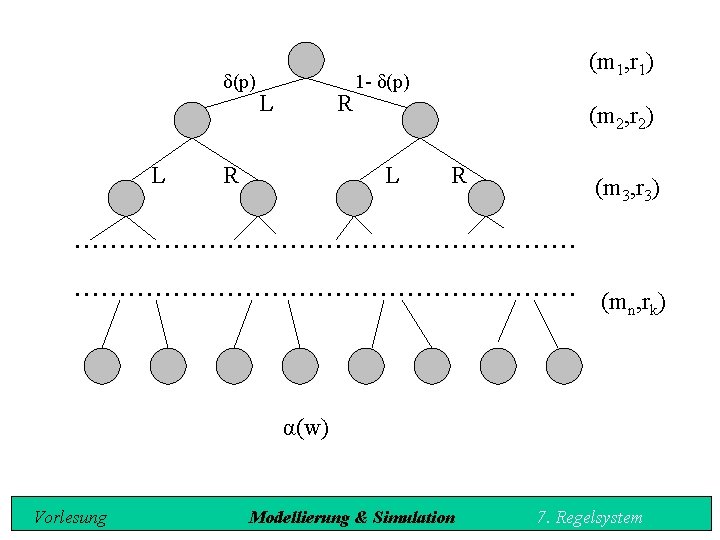
δ(p) L L R R (m 1, r 1) 1 δ(p) (m 2, r 2) L R (m 3, r 3) . . . . . . . (mn, rk) α(w) Vorlesung Modellierung & Simulation 7. Regelsystem

Gegeben sei ein metabolisches Basissystem G = (Z, R , z 0) mit: z 0 = {S 1} und R = {r 1, r 2, r 3} mit r 1 = (p 1, {S 1, Sx}, {S 2}, {E 1}, Æ), r 2 = (p 2, {S 1, Sx}, {S 2}, {Ex}, Æ) und r 3 = (p 3, {Sk}, {Sh}, {Ek}, Æ) und δ(p 1) = 3/4 =: p, δ(p 2) = 3/4 =: p‘, δ(p 3) = 1/5 =: p''. Sei z = {S 1, Sx, Sk, E 1, Ex, Ek} der aktuelle Zustand, dann ist die Liste der Paare (Gemisch, aktivierte Regel): ({S 1, Sx, E 1}, {r 1}) 1. Paar ({S 1, Sx, Ex}, {r 2}) 2. Paar ({Sk, Ek}, {r 3}) 3. Paar Vorlesung Modellierung & Simulation 7. Regelsystem
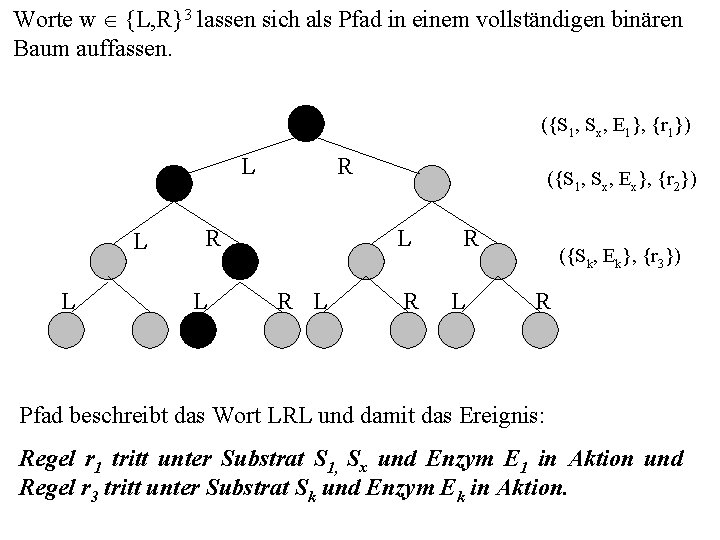
Worte w Î {L, R}3 lassen sich als Pfad in einem vollständigen binären Baum auffassen. ({S 1, Sx, E 1}, {r 1}) L L L R R L ({S 1, Sx, Ex}, {r 2}) L R R L ({Sk, Ek}, {r 3}) R Pfad beschreibt das Wort LRL und damit das Ereignis: Regel r 1 tritt unter Substrat S 1, Sx und Enzym E 1 in Aktion und Regel r 3 tritt unter Substrat Sk und Enzym Ek in Aktion.
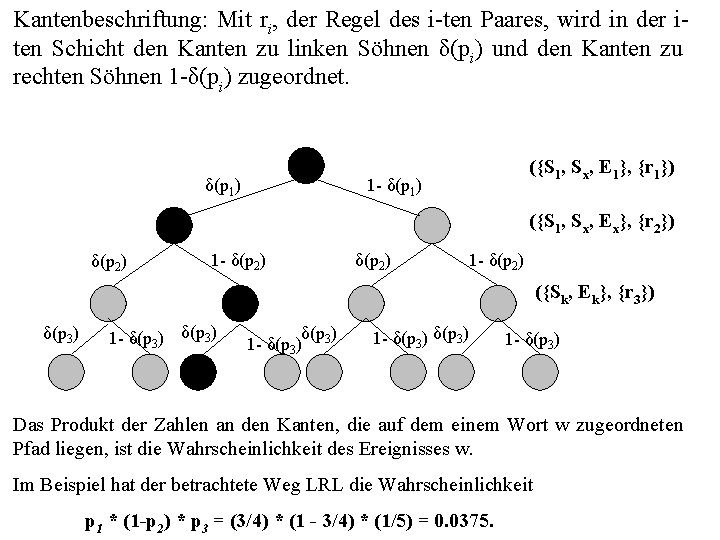
Kantenbeschriftung: Mit ri, der Regel des i ten Paares, wird in der i ten Schicht den Kanten zu linken Söhnen δ(pi) und den Kanten zu rechten Söhnen 1 δ(pi) zugeordnet. δ(p 1) ({S 1, Sx, E 1}, {r 1}) 1 δ(p 1) ({S 1, Sx, Ex}, {r 2}) δ(p 2) 1 δ(p 2) ({Sk, Ek}, {r 3}) δ(p 3) 1 δ(p 3) δ(p ) 1 δ(p 3) 3 1 δ(p 3) Das Produkt der Zahlen an den Kanten, die auf dem einem Wort w zugeordneten Pfad liegen, ist die Wahrscheinlichkeit des Ereignisses w. Im Beispiel hat der betrachtete Weg LRL die Wahrscheinlichkeit p 1 * (1 -p 2) * p 3 = (3/4) * (1 - 3/4) * (1/5) = 0. 0375.
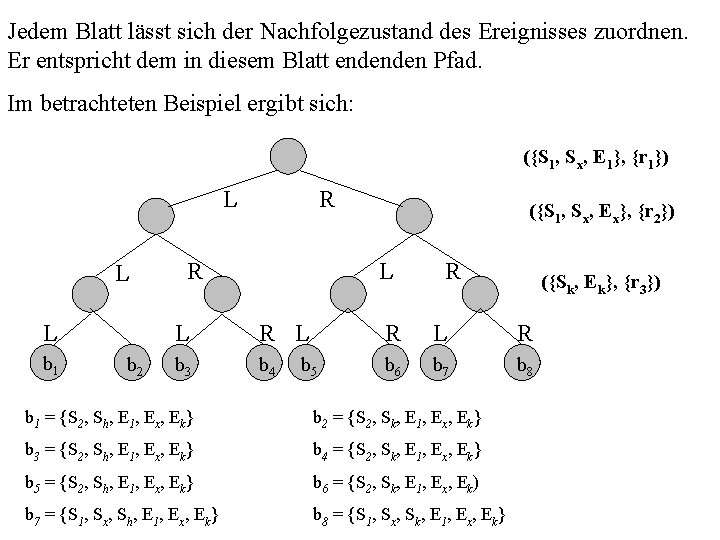
Jedem Blatt lässt sich der Nachfolgezustand des Ereignisses zuordnen. Er entspricht dem in diesem Blatt endenden Pfad. Im betrachteten Beispiel ergibt sich: ({S 1, Sx, E 1}, {r 1}) L L L b 1 b 2 R R ({S 1, Sx, Ex}, {r 2}) L R ({Sk, Ek}, {r 3}) L R L R b 3 b 4 b 6 b 7 b 8 b 5 b 1 = {S 2, Sh, E 1, Ex, Ek} b 2 = {S 2, Sk, E 1, Ex, Ek} b 3 = {S 2, Sh, E 1, Ex, Ek} b 4 = {S 2, Sk, E 1, Ex, Ek} b 5 = {S 2, Sh, E 1, Ex, Ek} b 6 = {S 2, Sk, E 1, Ex, Ek) b 7 = {S 1, Sx, Sh, E 1, Ex, Ek} b 8 = {S 1, Sx, Sk, E 1, Ex, Ek}

Mit dieser Sichtweise kann man jetzt ausrechnen, dass im obigen Beispiel gilt: P(b 1|z) = (3/4) * (1/5) = 0. 14 P(b 3|z) = (3/4) * (1 - (3/4)) * (1/5) = 0. 05 P(b 5|z) = (1 - 3/4) * (1/5) = 0. 05 Damit ergibt sich für {S 2, Sh, E 1, Ex, Ek} die Wahrscheinlichkeit 0. 24. Die Ereignisse in verschiedenen Generationen werden als unabhängige Ereignisse angesehen. Damit hat eine Ableitung A = (z 1, z 2, . . . , zh) die Wahrscheinlichkeit P(A): = P(z 2|z 1) * P(z 3|z 2). . . * P(zh|zh 1) Vorlesung Modellierung & Simulation 7. Regelsystem

Ebenso lässt sich die Wahrscheinlichkeit P(M, i), dass die Substanzmenge M nach i Generationen vorliegt, rekursiv bestimmen: 1 falls A = Æ P(A, 0) : = (I. ) 0 sonst P(A, i+1) : = SzÎZ P(A|z) P(z, i) (II. ) (I. ) Start Zellzustand erhält die Wahrscheinlichkeit 1. (II. ) Berücksichtigt, dass jeder Zustand auf verschiedenen Wegen erreicht werden kann. Es wird davon abstrahiert, mit welchen Schritten man den Zellzustand erreicht. Vorlesung Modellierung & Simulation 7. Regelsystem

Analytisch-metabolisches System Konzentrationen sollen Berücksichtigung finden. Kinetische Effekte im Modell. Metabolische Regel: 5 Tupel (p, V, N, F, H). Komponenten = Liste von Metabolite. Konzentrationswerte: Zähleinheit für die jeweiligen Metabolite ist die Anzahl der Moleküle. Gemisch: Menge von Metaboliten, die jeweils in unterschiedlicher Quantität vorliegen. Formal: Verallgemeinerte Multimengen. Vorlesung Modellierung & Simulation 7. Regelsystem

Multimenge Eine verallgemeinerte Multimenge m über einer Menge X ist eine Abbildung m: X ® Z (in die Menge der ganzen Zahlen). Beispiel: Sei X = {a, b, c} eine beliebige Menge. Eine mögliche Multimenge über X ist: m = {(a, 6), (b, 9), (c, 4)}. Vorlesung Modellierung & Simulation 7. Regelsystem

Multimenge Vereinbarung: Bezeichne MIN die Minimalfunktion und MAX die Maximalfunktion. Für zwei Multimengen m und u gilt: xÎm º m(x) > 0 uÍm º " xÎX u(x) £ m(x) uÇm º { (x, MIN(u(x), m(x)) : x Î X } uÈm º { (x, MAX(u(x), m(x)) : x Î X } u+m º { (x, u(x)+m(x) : x Î X } u m º { (x, u(x) m(x) : x Î X } m(x) : : = Anzahl eines Elementes x in einer Multimenge m Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Metabolisches Gemisch Sei z Í Z ein beliebiger Zellzustand und k eine Multimenge über Z. k heißt metabolisches Gemisch mit Zellzustand z, wenn z = { x : k(x) > 0 }. Im weiteren werden die metabolischen Gemische als Liste wie folgt dargestellt [k(x 1) x 1, . . . , k(xn) xn], wobei nur die Komponenten eingetragen werden, deren Werte verschieden von Null sind. Vorlesung Modellierung & Simulation 7. Regelsystem

Komponenten eines metabolischen Gemisches werden als Liste zusammengefasst. Der Wert Eins wird dabei im weiteren optional angewendet, d. h. er muss nicht explizit genannt werden. Beispiel: Sei z = {Glucose, Lactose, RNS Polymerase}, dann ist [34 Glucose, Lactose, 15 RNS Poly merase] ein metabolisches Gemisch, das sich aus 34 Einheiten Glucose, einer Einheit Lactose und 15 Einheiten RNS Polymerase zusammensetzt. Vorlesung Modellierung & Simulation 7. Regelsystem

Reaktionen basieren auf spezifischen Reaktionsgeschwindigkeiten, die sich aus der Konzentration der beteiligten Metaboliten ergibt. Definition: Metabolisches Einflussgemisch Sei n Î N, γ eine rationale Zahl aus dem Intervall [0; 1] und f eine berechenbare monotone Funktion. Für f ist das Intervall [0; 1] von rationalen Zahlen Definitionsbereich und Wertebereich. Der metabolische Einfluss des Metaboliten m ist ein 3 Tupel (f, n, γ). f ist die Einflussfunktion, n der Schwellenwert und γ die Stärke des Metaboliten m (Modifikationsfaktor). Ein metabolisches Einflussgemisch ist eine Liste von Metaboliten mit zugehörigem metabolischen Einfluss. Die Metaboliten heißen Hemmer oder Förderer. Vorlesung Modellierung & Simulation 7. Regelsystem

Schwellenwert = Sättigungsgrad des Metaboliten. Sei die aktuelle Konzentration des Metaboliten größer oder gleich diesem Schwellenwert Einflussfunktionliefertden. Wert 1 undder. Metabolitkann seine volle Wirkung ausüben, indem die Regel wahrscheinlichkeit mit der Stärke multipliziert wird. Sei die aktuelle Konzentration unterhalb des Schwellenwertes wird Es eine rationale Zahl aus dem Intervall [0; 1] in Abhängigkeit der gewählten Einflussfunktion ermittelt: sigmoide (s), hyperbolische (h) und lineare (l) Einflussfunktionen. Vorlesung Modellierung & Simulation 7. Regelsystem

Schwellenwert Im implementierten Simulationsprogramm findet die sigmoide (s), hyperbolische (h) und lineare (l) Funktion Berücksichtigung, indem der Benutzer für f abkürzend den jeweiligen Anfangsbuchstaben der gewünschten Funktion in das 3 Tupel einsetzt (f Î {l, s, h}). Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Analytisch-metabolische Regel Sei Z ein metabolisches Gemisch. Eine analytisch-metabolische Regel ist ein 5 Tupel (p, V, N, F, H) mit: p ist Regelwahrscheinlichkeit aus dem Intervall [0; 1], V positive Multimenge über Z (genannt Vorhergemisch), N positive Multimenge über Z (genannt Nachhergemisch), F förderndes metabolisches Einflußgemisch und H hemmendes metabolisches Einflußgemisch. Vorlesung Modellierung & Simulation 7. Regelsystem

Für eine analytisch metabolische Regel r bezeichnet VOR(r) das Vorhergemisch, NACH(r) das Nachhergemisch, FÖR(r) die Metaboliten des fördernden Einflussgemisches und HEM(r) die Metaboliten des hemmenden Einflussgemisches. Vorlesung Modellierung & Simulation 7. Regelsystem

Beispiel: Hydrolyse der Lactose ist ein enzymatisch gesteuerter Prozeß. Lactose wird in Galactose und Glucose umgesetzt. Katalyse: ß Galactosidase = Modell: Positives Einflußgemisch mit einer hohen Wirkung. Eine mögliche Regel: r= (1. 0, [Lactose], [Galactose, Glucose], [ß Galactosidase(s, 100, 0. 99)], Æ) mit: VOR(r) = {[Lactose]}, NACH = {[Galactose, Glucose]}, FÖR(r) = {[ß Galactosidase]} und HEM(r) = Æ. Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Analytisch-metabolisches System Das 3 Tupel G = (Z, R, k 0) mit Z Menge der Metabolitgemische, k 0 eine positive Mulitmenge über Z und R eine endliche Menge von analytisch metabolischen Regeln heisst analytisch metabolisches System. Jede Multimenge k über Z heißt Konfiguration des analytisch metabolischen Systems. k 0 heißt Start-Konfiguration von G. Vereinbarung: Vorlesung K = Menge aller Konfigurationen des Systems. Modellierung & Simulation 7. Regelsystem

Formalismus: Einfluss der Hemm Substanzen und Förder Substanzen in Abhängigkeit der aktuellen Konfiguration und der jeweiligen Einflussgemische unabhängig voneinander berechnen. Idee: Vorlesung Einflusswerte multiplikativ mit der Regelwahrscheinlichkeit verrechnen. Modellierung & Simulation 7. Regelsystem

Definition: Modifizierte Regelwahrscheinlichkeit. Sei r = (p, V, N, F, H) eine analytisch metabolische Regel. Sei e ein Metabolit, der Förder Substanz oder Hemm Substanz ist, mit dem metabolischen Einfluss (fe, ne, γe). Der wirksame Einfluss auf die Regel r in der Konfiguration z ist γe, falls der Schwellenwert ne überschritten ist, d. h. z(e) > ne. Andernfalls bestimmt er sich durch γe = f(z(e)/ne). Der gemeinsame Einfluss der Förderer (γFÖR(r)) bestimmt sich durch: SeÎFÖR(r) (γe * e) / SeÎFÖR(r) γe. Der Einfluß der Hemmer (γHEM(r)) ist durch MAXeÎHEM(r) e gegeben. Die modifizierte Regelwahrscheinlichkeit ergibt sich dann aus: modp(r, k) = p * γFÖR(r) * γHEM(r). Vorlesung Modellierung & Simulation 7. Regelsystem
![Beispiel r=(0. 9, [A, B], [C], [F 1(l, 10, 1. 0), F 2(s, 10, Beispiel r=(0. 9, [A, B], [C], [F 1(l, 10, 1. 0), F 2(s, 10,](http://slidetodoc.com/presentation_image_h2/4a054bf4da6d7e3dd5df4ee50ec1bc21/image-37.jpg)
Beispiel r=(0. 9, [A, B], [C], [F 1(l, 10, 1. 0), F 2(s, 10, 0. 1)], [H 1(l, 10, 1. 0), H 2(s, 10, 0. 9)]) eine analytisch metabolische Regel und [A, B, 5 F 1, 20 F 2, 10 H 1] die aktuelle Konfiguration. Dann ergeben sich die folgenden Modifikationsfaktoren: für F 1 = 0. 5, F 2 = 0. 09 und H 1 = 0. 0. Daraus ergibt sich die modifizierte Regelwahrscheinlichkeit modp(r) = 0. 0, weil die Hemm Substanz H 1 absolut wirkt. Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Aktivierung Sei G = (Z, R, k 0) ein analytisch metabolisches System und k eine Konfiguration des Systems. Für die Aktivierung der Regel r unter k gilt: a) Ist eine Komponente der Konfiguration k negativ, so ist r nicht aktiviert. b) Sei k eine positive Multimenge, dann heißt r = (p, V, N, F, H) unter k aktiviert, wenn es gilt: V Í k und modp(r, k) > 0. AKT(k) = { r Î R : r ist aktiviert unter der Konfiguration k } bezeichnet die Menge aller aktivierten Regeln unter der Multimenge k. Gilt AKT(k) = Æ, dann terminiert G in der Konfiguration k. Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Aktion Sei G = (Z, R, k 0) ein analytisch metabolisches System. r = (p, V, N, F, H) eine aktivierte Regel in der Konfiguration k. Dann ist die Aktion von r, in Symbolen k ® k', gegeben durch: k' = (k - VOR(r)) + NACH(r). Vorlesung Modellierung & Simulation 7. Regelsystem

Beispiel: G = (Z, R, k 0) ein analytisch metabolisches System. k = [H 1, 2 A] sei die aktuelle Konfiguration R = {r 1, r 2} mit r 1 = (0. 5, [A], [B, 2 C], [E], [H 1, H 2]) und r 2 = (0. 8, [A], [B], [E], [H 2]). Regel r 1 nicht aktiviert, weil der Repressor H 1 anwesend ist. Regel r 2 aktiviert, weil H 2 nicht und Enzym E 1 anwesend ist. Aktion der Regel r 2 führt zu Vorlesung k' = [H 1, 2 A] - [A] + [B] = [H 1, A, B]. Modellierung & Simulation 7. Regelsystem

Einschritt-Ableitung: ‚Quasi' gleichzeitige Aktion aktivierter Regeln. Definition: Nachfolgekonfiguration - Einschritt-Ableitung Sei G = (Z, R, k 0) ein analytisch metabolisches System und k eine beliebige Konfiguration für die gilt: T Í AKT(k) mit AKT(k) ¹ Æ. Die 'quasi' gleichzeitige Aktion der Regelmenge T heißt Einschritt-Ableitung und führt zur Nachfolgekonfiguration k', in Symbolen k T k', wenn gilt k' = (k - S"tÎT VOR(t)) + S"tÎT NACH(t). Wir sagen k wird mittels der Aktion T nach k' überführt. D(k) = { k' : $ TÍAKT(k) Nachfolgekonfigurationen. Vorlesung k T k' } beschreibt die Menge aller Modellierung & Simulation 7. Regelsystem

Beispiel: Gegeben ein analytisch metabolisches System G mit k = [6 A, 8 B, 3 E] und der Regelmenge R mit r 1 = (0. 8, [2 A], [3 B], [E], [X]) und r 2 = (0. 5, [2 B], [3 D], [E], [X]). Dann gilt: D(k) = AKT(k) = {r 1, r 2} und {[6 A, 8 B, 3 E], [4 A, 11 B, 3 E], [6 A, 6 B, 3 D, 3 E], [4 A, 9 B, 3 D, 3 E] } ergibt sich unmittelbar aus den möglichen Einschritt Ableitungen. Sei k' = [5 U, 14 H], dann ist AKT(k') = Æ. In diesem Fall terminiert G in dieser Konfiguration. Vorlesung Modellierung & Simulation 7. Regelsystem

Definition: Ableitung Sei G = (Z, R, k 0) ein beliebiges analytisch metabolisches System. Eine Folge von Konfigurationen k 1, . . . , kn+1 (nÎN) heißt Ableitung von k 1 nach kn+1 mittels der Aktion T 1, . . . , Tn, wenn gilt: i=1, . . . , n ki ÞTi ki+1. Ferner ist die n Schritt Ableitung k n k' definiert, in Worten k ist in n Schritten nach k' ableitbar, wenn gilt: Es gibt Konfigurationen k 1, . . . , kn+1 und Aktionen T 1, . . . , Tn, so dass Aktionen T 1, . . . , Tn. Ferner ist k * k', in Worten k ist ableitbar nach k', wenn es ein n gibt, so dass k n k' gilt. ABL(G) = { k : k 0 * k } bezeichnet die Menge aller aus k 0 ableitbaren Konfigurationen. Vorlesung Modellierung & Simulation 7. Regelsystem

Beispiel: Betrachtet wird das analytisch metabolische System s. o. Dann ist eine mögliche Ableitung gegeben durch: [6 A, 8 B, 3 E] ÞT [4 A, 11 B, 3 E] ÞT' [2 A, 12 B, 3 D, 3 E] ÞT'' [15 B, 3 D, 3 E] mit T = {r 1}, T' = {r 1, r 2} und T''= {r 1}. In G ist die Konfiguration [15 B, 3 D, 3 E] durch die Ableitung [6 A, 8 B, 3 E] * [15 B, 3 D, 3 E] erreichbar. Vorlesung Modellierung & Simulation 7. Regelsystem

Beispiel: Sei G = (Z, R, k 0) ein analytisch metabolisches System mit k = [X] und R = {r 1, r 2, r 3} mit r 1 = (1. 0, [X], [B], Æ, Æ), r 2 = (1. 0, [B] , [C], Æ, Æ) und r 3 = (1. 0, [X], [D], Æ, Æ). Unter k ist T = {r 1, r 3} aktiviert. Die Nachfolgekonfiguration von k unter T ergibt: k' = [X] ([X] + [X]) + ([B] + [D]) = [-X, B, D] Vorlesung Modellierung & Simulation 7. Regelsystem
- Slides: 45